稻瘟病菌LAMP检测引物组及应用的制作方法
本发明涉及植物病害快速预警技术,属于植物保护学科中的病害预测预报研究与应用领域。
背景技术:
稻瘟病是我国各水稻产区最主要的病害之一,在水稻整个生育期均可发生,对水稻的产量和品质均可造成严重的影响。特别是穗瘟往往会造成田间出现大量枯白穗,甚至绝收。若不能适时有效的施用化学农药,不仅难以控制病害的发生,还会因大量频繁的使用化学农药而使病原菌产生抗药性,并导致农药残留和对环境的污染。对病害的精准预报是适时施药和有效控病的基础,但已有的病害预测预报方式主要靠专家在田间系统的大面积调查,然后根据经验发表病害情报,不仅费时费力,且因整合多地资料也需要时间,再加上栽培方式的多样化,各田块作物的生育期并不一致,从而导致生产上经常出现过早或过迟施用农药的现象,防病效果并不理想。因此,发展快速实时的病害预测预报方法,对指导农民用药,有效控制病害具有重要意义。
lamp技术是特定的针对病原物靶基因的某区域设计特异引物,在链转换dna聚合酶的作用下,特异、痕量检测样品中的dna。该方法操作简单、特异性强、产物易检测,且不需要昂贵的试剂和精密高质的仪器,在作物病害早期预警上有广阔的应用前景。
技术实现要素:
本发明的目的是提供一种快速检测稻穗中稻瘟病菌带菌率的技术,对稻瘟病的发生与防控进行实时预警。本发明中,基于稻瘟病菌bt1基因序列利用在线软件primerexplorerv设计的引物组具有特异高效扩增稻瘟病菌的特性,可检测未显症稻穗的带菌率,根据带菌率与后期病害严重度的相关性,可对稻穗瘟的发生作物实时预警。
本发明公开了一组稻瘟病菌lamp检测引物,该组引物组成如下:
btf3-19:5′-acgtccagaacaagaactcg-3′(seqidno.19)
btfip-19:5′-ctgctgtagaactccggcccccaacaacatccagacc-3′(seqidno.24)
btbip-19:5′-ggatggcagtcgagtttccgatcactcgtcaagtgacggta-3′(seqidno.31)
btb3-19:5′-caagtccgcgttccgaaa-3′(seqidno.32)。
本发明所述引物组能特异检测稻瘟病菌基因组dna。
本发明还公开了上述引物组在稻瘟病实时预警上的应用。
本发明还公开了一种稻瘟病菌lamp检测方法。
引物组合19是根据稻瘟病菌bt1基因序列设计的可专化性扩增稻瘟病菌基因组dna的特异引物,对水稻其它病原菌无扩增条带。该检测反应的最优条件为63℃下反应40min,在此反应条件下可检测到的稻瘟病菌dna量可达pg级。利用此引物组和反应条件,检测得的稻穗带菌率与后期病害严重度呈显著正相关,相关系数达0.7395~0.9194,说明该方法可以用于田间稻瘟病的实时预警。
附图说明
图1不同btf3/btb3引物对扩增稻瘟病菌dna产物电泳图。
图2qpcr方法检测引物对的灵敏度
图3qpcr方法检测引物对的特异性。
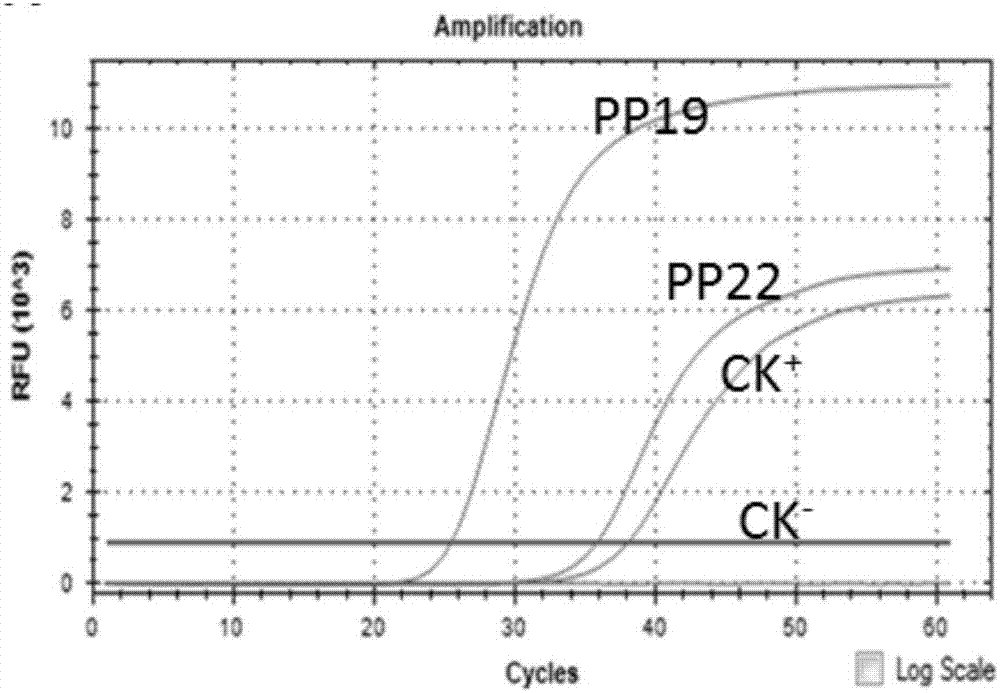
图4引物组19对稻瘟病菌dna的lamp检测反应。pp19和pp22分别表示引物对19和引物对22。
图5qpcr和lamp方法检测灵敏度比较;a:qpcr方法,1~6分别表示dna底物梯度浓度为5.9×102~5.9×10-3ng;b:lamp方法,a~g分别表示dna底物梯度浓度为5.9×102~5.9×10-4ng。
图6lamp检测带菌率与田间后期稻穗瘟病穗率相关性。a:2015年,b:2016年。
具体实施方式
1、特异性引物的设计与筛选
(1)根据稻瘟病菌bt1基因序列(登录号:xm_003718381),利用在线软件primerexplorer设计lamp检测引物组,选择其中23组引物进行特异性测定(表1)。
表1据稻瘟病菌bt1基因序列设计的部分lamp引物组
(2)用23对btf3/btb3引物对稻瘟病菌基因组dna进行pcr扩增,共有9对引物可以从稻瘟病菌中扩增出单一条带,且扩增效果较好的为第19对(btf3-19(seqidno。19)/btb3-19(seqidno。24))和第22对(btf3-22(seqidno。25)/btb3-22(seqidno。30))引物(图1)。
2、特异性与灵敏度检测
(1)qpcr结果表明,引物对btf3-19/btb3-19在进行24个循环后就可以检测到病原菌dna,而引物对btf3-22/btb3-22需进行34个循环左右(图2)。
(2)用水稻其它常见病原菌如水稻纹枯病菌(rhizoctoniasolnai)、恶苗病菌(fusariumfujikuroi)和稻曲病菌(ustilaginoideavirens)等来检测引物对btf3-19/btb3-19的专化性发现,引物对btf3-19/btb3-19只能对稻瘟病菌dna进行扩增,其它几种菌均表现阴性,说明引物对btf3-19/btb3-19可以用来进行稻瘟病菌dna的特异性检测(图3)。
(3)用引物组19(btf3-19/btfip-19/btbip-19/btb3-19)进行lamp检测,加入稻瘟菌dna的pcr管呈现绿色(阳性),而加入水稻纹枯病菌dna和稻曲病菌dna的pcr管显褐色(阴性)(图4)。
fip和bip是primerexplorer中对引物的特定命名,fip为引物f1c和f2序列的结合,bip是b1c和b2序列的结合。f1c是f1的互补序列,b1c为b1的互补序列。所以依据表1,btfip-19及btbip-19序列如下:
btfip-19:5′-ctgctgtagaactccggcccccaacaacatccagacc-3′(seqidno.31)
btbip-19:5′-ggatggcagtcgagtttccgatcactcgtcaagtgacggta-3′(seqidno.32)
(4)将浓度为5.9×102ng的稻瘟病菌基因组dna进行梯度稀释后,分别进行qpcr和lamp检测,结果表明lamp检测灵敏度可达到5.9pg/ml(管a到管f均显示绿色,仅管g显示褐色,图5b),比qpcr灵敏度高10倍(图5a)。
3、该技术在稻穗瘟病预警上的应用
于2015和2016年在同一地区分别于6块不同田块中取始穗期稻穗100穗,检测其带菌率,30d后5点取样法调查各田块病穗率,每点100穗。结果表明,经lamp检测的稻穗带菌率与后期田间病穗率呈显著正相关,尽管2016年田间发病较轻,但相关性趋势仍然一致,说明该种方法可用于稻穗瘟的预警(图6)。
sequencelisting
<110>扬州大学
<120>稻瘟病菌lamp检测引物组及应用
<130>
<160>32
<170>patentinversion3.3
<210>1
<211>19
<212>dna
<213>人工序列
<400>1
acctgctctgccatcttgt19
<210>2
<211>20
<212>dna
<213>人工序列
<400>2
accatgaccacatccacatg20
<210>3
<211>21
<212>dna
<213>人工序列
<400>3
ctatggtggtgtcggcacctt21
<210>4
<211>22
<212>dna
<213>人工序列
<400>4
aggtctccatgaaggaggtcga22
<210>5
<211>19
<212>dna
<213>人工序列
<400>5
tgagcagcatgaagcagct19
<210>6
<211>20
<212>dna
<213>人工序列
<400>6
ctaggggttgttgtaggtct20
<210>7
<211>18
<212>dna
<213>人工序列
<400>7
agccgtggaaaggtctcc18
<210>8
<211>18
<212>dna
<213>人工序列
<400>8
aggaggtcgaggaccaga18
<210>9
<211>22
<212>dna
<213>人工序列
<400>9
atgaagcagctcacctaggggt22
<210>10
<211>22
<212>dna
<213>人工序列
<400>10
agaccgctctctgctctatccc22
<210>11
<211>19
<212>dna
<213>人工序列
<400>11
agtagcctttgagctgacg19
<210>12
<211>18
<212>dna
<213>人工序列
<400>12
ggtcctcgacaagttcgc18
<210>13
<211>20
<212>dna
<213>人工序列
<400>13
agtggatccccaacaacatc20
<210>14
<211>19
<212>dna
<213>人工序列
<400>14
cagaccgctctctgctcta19
<210>15
<211>22
<212>dna
<213>人工序列
<400>15
tagcctttgagctgacggtagg22
<210>16
<211>21
<212>dna
<213>人工序列
<400>16
ggagctgttcaagcgtgtcgg21
<210>17
<211>20
<212>dna
<213>人工序列
<400>17
cgtaaccatgtgaccactcc20
<210>18
<211>20
<212>dna
<213>人工序列
<400>18
cctgctctacctcaagtgac20
<210>19
<211>20
<212>dna
<213>人工序列
<400>19
acgtccagaacaagaactcg20
<210>20
<211>19
<212>dna
<213>人工序列
<400>20
ccccaacaacatccagacc19
<210>21
<211>18
<212>dna
<213>人工序列
<400>21
gccggagttctacagcag18
<210>22
<211>22
<212>dna
<213>人工序列
<400>22
atcggaaactcgactgccatcc22
<210>23
<211>19
<212>dna
<213>人工序列
<400>23
cactcgtcaagtgacggta19
<210>24
<211>18
<212>dna
<213>人工序列
<400>24
caagtccgcgttccgaaa18
<210>25
<211>18
<212>dna
<213>人工序列
<400>25
gcgcaacgtccagaacaa18
<210>26
<211>19
<212>dna
<213>人工序列
<400>26
gtcgagtggatccccaaca19
<210>27
<211>18
<212>dna
<213>人工序列
<400>27
gccggagttctacagcag18
<210>28
<211>22
<212>dna
<213>人工序列
<400>28
atcggaaactcgactgccatcc22
<210>29
<211>19
<212>dna
<213>人工序列
<400>29
cactcgtcaagtgacggta19
<210>30
<211>18
<212>dna
<213>人工序列
<400>30
caagtccgcgttccgaaa18
<210>31
<211>37
<212>dna
<213>人工序列
<400>31
ctgctgtagaactccggcccccaacaacatccagacc37
<210>32
<211>41
<212>dna
<213>人工序列
<400>32
ggatggcagtcgagtttccgatcactcgtcaagtgacggta41
- 还没有人留言评论。精彩留言会获得点赞!
- 水稻稻瘟病抗性基因Pi2‑1的分子标记方法及应用与流程
- 一种稻瘟病抗性基因Piz‑t功能特异性分子标记及其检测方法和应用与流程
- 一种接种架及稻瘟病菌接种系统的制作方法与工艺
- 谷梅4号抗稻瘟病基因Pigm的分子标记及其应用的制作方法与工艺
- 水稻稻瘟病抗性基因Pita、Pib分子标记方法与流程
- 一种基于猪非典型瘟病毒E2基因的荧光定量RT‑PCR检测试剂盒的制作方法与工艺
- 稻瘟病菌LAMP检测引物组及应用的制造方法与工艺
- 一种制备稻瘟病菌促分裂原活化蛋白激酶MoMps1晶体的方法与流程
- 水稻抗稻瘟病Pi9基因的共显性功能分子标记Pi9InDel1及其应用的制造方法与工艺
- 水稻抗稻瘟病Pi9基因的共显性功能分子标记Pi9InDel2及其应用的制造方法与工艺