一组用于辅助鉴别蒙古系绵羊中的纯种湖羊的SNP标记、引物及应用的制作方法
本发明属于动物分子育种技术领域,具体涉及一种辅助鉴别蒙古系绵羊中的纯种湖羊的snp标记组合、引物及应用。
背景技术:
中国地方绵羊可以分为两个遗传群:瘦尾型(藏系绵羊)和肥尾型(蒙古系绵羊和哈萨克系绵羊)群体。其中蒙古系绵羊包含了乌珠穆沁羊、苏尼特羊、小尾寒羊、广灵大尾羊、滩羊、湖羊等优秀的地方品种。
湖羊作为我国宝贵的地方绵羊品种,具有全年发情,性成熟早,早期生长速度快,肉质好等特征,是国际上稀有的高产绵羊品种。此外,湖羊还对炎热潮湿多雨的环境表现出较强的适应性,性情温顺适合舍饲,使得该品种在南方地区被广泛饲养。在生产过程中,湖羊通常被用作一种优秀的母本与其他蒙古羊品种杂交,以提高后代的生长性能。但这种生产方式导致湖羊长期处于杂交、混交状态,而在4种繁育组合中纯繁的机率只占1/4,相反产生杂合后代的概率是纯繁的3倍,进一步压缩了纯繁群体的数量。上个世纪末,随着杂合群体的逐渐扩散,纯种湖羊在人们的视觉和记忆中渐渐模糊淡化,将纯种与杂合个体全部泛称为湖羊。此外,蒙古系绵羊及其杂交后代间较为相似的体型外貌,导致人们难以鉴别蒙古系绵羊中的纯种湖羊,并最终产生了在育种过程中将其他蒙古羊系绵羊或其与湖羊的杂交后代错当湖羊使用的情况。这对于目前湖羊原种的认定和遗传资源的保护与开发利用都十分不利。
现在,不论是湖羊的保种还是遗传资源的开发利用,都离不开对纯种湖羊的鉴别。通常情况下,品种鉴别都采用观察其体形外貌、肤色、行为习性等不同表型的方法。虽然该方法具有方便快捷,时效性高,成本低的优点,但该方法缺少量化指标且对从业人员的经验要求较高,不同水平的人员和个体差异将导致鉴别准确率显著不同,且蒙古系绵羊及其杂交后代与纯种湖羊外貌相似,亲缘相近的特性又进一步降低了外貌鉴别的准确性。为了解决这些问题,从遗传分子的层面进行辅助鉴别的方法受到了越来越多的重视。
dna鉴别技术的产生源于dna的遗传与变异。用于dna鉴别的分子标记包括rflp(核酸限制性片段长度多态性)标记、rapd(随机引物扩增多态性)标记、aflp(扩增片段长度多态性)标记、ssr(简单序列重复)标记和snp(单核苷酸多态性)标记。其中rflp标记不安全检测灵敏度也不够高。rapd标记的技术简单,检测速度快,但是实验重复性和可靠性较差,难以推广。aflp标记有较高的稳定性,但对基因组纯度和反应条件高,不适合产业应用。而ssr标记相比与snp标记虽然等位基因众多,多态丰富,但也随之产生了带型复杂,识别自动化和规模化困难的问题。
snp标记是第3代分子标记,基于基因组同一位点上单个核苷酸的变异设计,这种差异包括单个碱基的置换、颠换、缺失和插入,但通常发生的只有置换和颠换,二者发生之比为2:1,并且通常以二等位基因的形式存在。snp标记分布广泛,遗传稳定,可帮助区分两个个体遗传物质的差异,被认为是应用前景最好的遗传标记。
目前为止,育种工作者发掘出了大量有关湖羊多羔、毛色等性状的snp标记,如fecb位点,但是大多数标记在湖羊和其他品种间不具有特异性,难以用来鉴别和筛选纯繁群体。
技术实现要素:
本发明的目的是利用snp标记易检测,成本低的优点,建立了一套用于蒙古羊和湖羊杂交群体中辅助鉴别纯种湖羊的snp标记组合,并提供用于鉴别纯种湖羊snp标记组合的引物及应用,以解决现有湖羊纯繁后代与蒙古羊和湖羊的杂交后代不易分辨、选种困难的问题。
所述的含有本发明的snp标记组合的核苷酸序列如seqidno:1和seqidno:2所示,所述的六个snp标记分别位于seqidno:1的第196,310,423,425位和seqidno:2的第563,636位。所述第一、第二、第三、第四snp标记位于seqidno:1所示核苷酸序列的方框标记处;所述第五、第六snp标记位于seqidno:2所示核苷酸序列的方框标记处。
上述的snp标记组合进行纯种湖羊辅助鉴别的方法,包括以下步骤:(1)通过体型外貌初步鉴定绵羊群体;(2)采集该绵羊群体的血液组织样品并提取基因组dna;(3)用已提取的基因组dna为模板,使用权利要求2所述的引物对进行pcr扩增;(4)扩增产物进行测序,分析测序结果,判读seqidno:1的第196,310,423,425位点和seqidno:2的第563,636位点的多态性。
根据本发明的实施例,所示seqidno:1和seqidno:2核苷酸序列中,在纯种湖羊中snp标记组合均为纯和型,而其它绵羊snp标记组合均是杂合型。具体地,纯种湖羊在本发明所述的snp标记组合的基因型均为纯和型,即cc,cc,cc,gg,cc,aa;其它绵羊品种在本发明所述的snp标记组合的基因型存在杂合型,即cg,cg,ca,ga,ct,ac。因此,本发明的snp标记组合,能够有效用于辅助鉴别纯种湖羊,进而能够高准确性地辅助选育纯种湖羊。
应用本发明公开的方法,对6个品种样品(每个品种48个样品)进行的纯种湖羊检测,准确率为99.89%。
附图说明
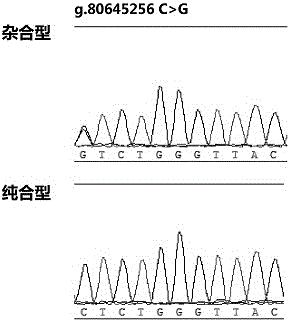
图1-6为本发明的六个snp标记位点的测序结果,杂合型的六个位点均是双峰,纯合型的六个位点均是单峰。杂合型的个体不是纯种湖羊,纯种湖羊的六个位点均是纯合型。
图7为本发明的两对引物扩增结果电泳图。第一列为marker,第二列为seqidno:1(809bp),第三列为seqidno:2(889bp)。
具体实施例
以下结合实施例,对本发明的具体实施方式进行详细描述,实施例用于说明本发明,但不用来限制本发明的范围。
实施例1
1.实验动物
分别随机采集乌珠穆沁羊、苏尼特羊、小尾寒羊、滩羊、湖羊、广灵大尾羊各48头的血液样本5ml,加入乙二胺四乙酸抗凝,带回实验室放入-20℃低温保存备用。
2.目的片段的pcr扩增和测序
使用苯酚氯仿法提取样本基因组dna作为反应模版,根据上述方法所设计的引物,进行pcr扩增:取dna模板1μl、seqidno3和seqidno4,seqidno5和seqidno6所示的引物各1μl、pcrmix试剂10μl、双蒸水7μl;其中所述dna模板浓度为30ng/μl,所述引物的浓度为10mol/l,所述pcrmix试剂为上海翊圣生物技术有限公司的h47160型号试剂;pcr扩增的反应程序为:预变性95℃5min、变性94℃50s、退火58.7℃(第一对引物)和60.1℃(第二对引物)40s、延伸72℃40s35个循环、延伸72℃5min。
pcr产物在2%的琼脂糖凝胶中电泳检测,扩增的目的片段大小约为900~1000bp,电泳图见图7,将剩余的扩增产物进行测序。
3.统计分析
使用lasergene软件将测序结果与模版片段序列比对、分析,判读g.80645256,g.80645470,g.80645483,g.80645486,g.80661032,g.80661105六个核苷酸位点的基因型。
如图1-6所示的g.80645256,g.80645470,g.80645483,g.80645486,g.80661032,g.80661105六个核苷酸位点的测序图。测序结果表明,这六个位点存在碱基突变(c>g,c>g,c>a,g>a,c>t,a>c)。这六个突变在所检测的6个品种中,纯种湖羊不存在多态性。
分析该snp位点等位基因的分布情况发现,纯种湖羊中g.80645256,g.80645470,g.80645483,g.80645486,g.80661032,g.80661105六个核苷酸位点都表现为纯合,基因型分别为cc,cc,cc,gg,cc,aa,而在其他品种群体中存在多态性。用该方法检测其是否为纯种湖羊的准确率为99.89%。
实施例2
1.实验动物
采集湖北宜昌致清和农牧有限公司200头种用湖羊的血液样本5ml,加入乙二胺四乙酸抗凝,带回实验室放入-20℃低温保存备用。
2.目的片段的pcr扩增和测序
使用苯酚氯仿法提取样本基因组dna,用已提取的dna为模版,根据上述方法所设计的引物,以相同的方法检测200头种用湖羊的基因型。
3.统计分析
使用lasergene软件将测序结果与模版片段序列比对、分析,判读g.80645256,g.80645470,g.80645483,g.80645486,g.80661032,g.80661105六个核苷酸位点的基因型,检测结果表明200头种用湖羊六个位点的基因型均为cc,cc,cc,gg,cc,aa,不存在杂合基因型个体。
序列表
<110>湖北多羔生物育种科技有限公司
<120>一组用于辅助鉴别蒙古系绵羊中的纯种湖羊的snp标记、引物及应用
<140>201811239944.9
<141>2018-10-23
<160>6
<170>siposequencelisting1.0
<210>1
<211>809
<212>dna
<213>绵羊(ovisaries)
<400>1
aagcattttgaagttgggttgggaagggcctcatgccatttataatgatactaaaaaact60
tgcataatttcattttgctattttcttttcagcttgatttttatctacgtgcctccttct120
ctacacaaagggctgcaaaccagaagctgtcctgcattcttgcttcaagcagaatgaaat180
ctcctacactcctctctctgggttacatgttcctggtcctgcttttcttccagcaggcct240
gggctcagttcccgagagagtgcgctaccattgaggctttgaggaatggcgtgtgttgcc300
cagacctgtccccactgtctgggcctgggtctgaccgctgcggtttctcatcagggaggg360
gtagatgtgaggtggcgatagccgactcccggccccacagccaccactacccacatgatg420
gccgagacgaccgagaggcctggcccacacgcttcttcaacaggacatgccgctgcagtg480
gcaatttctcaggacacaactgtggaacctgccgccctggctggggaggggctgcctgtg540
accagagggttctcacaggtaagcggagactgaatggatgcatagtcctgcatggaacgc600
aacacatttaatattgcagaccttcaaatcagttgaggtttaagaactcctagaaattgt660
aaaattcaagcctcacttttcatagctgaggaaactgaggcttagagaagctaagaaatg720
tatttaaggagttgaagttgaaactcaggtcttctgactaataacatttcctttcacaag780
atttgttgagcaacccctttataatagga809
<210>2
<211>889
<212>dna
<213>绵羊(ovisaries)
<400>2
agccctgtaaaatatgccctgtgtaatatactcttatttttctactacatgaacgtgctt60
ctagttgtttatcttaaaagagatgaagtgagacactctgagctgttttttgagaggtta120
tgaaatccaaaatctcctggtttaattttaaatccttttcttaaccaaggcaatggggta180
cagtggaagagcacagaattggatcctgaaagatctgggctccaaaaccagctccaccgt240
ctattaaccaaatgaccttgggcaagtgatttaaacactgagccatcatctcctcacctt300
cagaagagatataataactatcccaataggatgcagtcattatgagaaactggggagtgc360
tttgaagatcccaggtgctataaaggcaatgtggccaataaaaattaaatacgaggattt420
cgtcaagtacctggaacaatgcctacatttaggggatccaattttggcaacgattttact480
atttattttttgttctcattttattttcaaacaggtcggagttttagcattcctgagatt540
gtcaccatagcagtagtggctgcgttattactgatcgcggtcatttttgcgggcgcctct600
tgtctgattcgtgccagaagcaacatggatgaagcaaatcagcctctccttactgatcag660
tatcaacactacattgaagaaaatgaaaaaatccataatcctaatcagtctatggtctaa720
tgacaagtgtaaattctcatatgcatttgaatcataaaaaccacacacttagaacataat780
aggttgagttactaactgtattttcttttactctgttacttccttccttgtgcatgtcca840
tattggaattacaatctccagatattattttccagaactggggaaagtc889
<210>3
<211>20
<212>dna
<213>绵羊(ovisaries)
<400>3
aagcattttgaagttgggtt20
<210>4
<211>23
<212>dna
<213>绵羊(ovisaries)
<400>4
tcctattataaaggggttgctca23
<210>5
<211>22
<212>dna
<213>绵羊(ovisaries)
<400>5
agccctgtaaaatatgccctgt22
<210>6
<211>24
<212>dna
<213>绵羊(ovisaries)
<400>6
aagattgtgactttccccagttct24
- 还没有人留言评论。精彩留言会获得点赞!