可结合PD-L1的多肽及其应用的制作方法
本发明涉及生物医药领域。更特别地,涉及一种可结合pd-l1的多肽,所述的多肽在检测pdl1或治疗肿瘤或传染病中的应用。
背景技术:
肿瘤是指机体局部组织的细胞异常增生而形成的一种新生物,常常表现为局部的肿块。根据肿瘤的性质,一般将其分为良性肿瘤和恶性肿瘤。恶性肿瘤生长较快,易向周围组织扩散,容易发生转移,危及生命。pd-1(programmeddeath-1)蛋白是t细胞表面的一种重要的免疫抑制跨膜蛋白,为cd28超家族成员。一些肿瘤细胞能够表达pd-l1或者pd-l2与t细胞表面的pd-1结合,使pd-1的胞内结构域的酪氨酸磷酸化,抑制tcr信号通路,从而逃避t细胞的杀伤。因此,理论上可通过使用pdl1抑制剂例如抗pdl1抗体来对抗该免疫逃避机制,从而达到治疗这类肿瘤的目的。
1993年,一种来源于骆驼科的新型天然抗体被发现。该抗体天然缺失轻链而只由重链组成,其重链包含两个恒定区(ch2和ch3)、一个铰链区和一个重链可变区(variableheavychaindomain,vhh,即抗原结合位点),该重链可变区的相对分子质量约为13kda,仅为常规抗体的1/10,且分子高度和直径均在纳米级别,是目前可获得的最小的功能性抗体片段,因此又被称为纳米单抗(nanobody,nb)。因纳米单抗稳定性高(90℃条件下仍不会降解)、亲和力高、与人源抗体同源性超过80%、毒性和免疫原性均较低等特点,最近纳米单抗被广泛用于免疫诊断试剂盒研发、影像学研发以及针对肿瘤、炎症、传染病和神经系统疾病等领域的抗体药物研发。
目前已有一些抗pdl1抗体作为二线药物用于治疗某些肿瘤或者用于检测是否表达pdl1以作为用药参考或预后指标。鉴于目前抗体在患者中应答率较低等原因,因此我们期望通过新的技术手段,获得更为高效稳定的抗pdl1抗体。
技术实现要素:
本发明通过用抗原免疫骆驼,获取骆驼源纳米单抗及其vhh,用于诊断和治疗pd-l1适应症病人。基于这些研究,本发明提供了一种可结合pd-l1的多肽,包括3个互补决定区cdr1-3,cdr1序列为或包括seqidno:1-34所示序列之一,cdr2序列为或包括seqidno:35-63所示序列之一,cdr3序列为或包括seqidno:64-100所示序列之一。
在一个具体实施方案中,所述多肽还包括4个框架区fr1-4,所述fr1-4与所述cdr1-3交错排列。例如,可将fr1-4序列设计为如seqidno:101-104所示,但本发明的范围不限于此,也可将框架区fr1-4序列人源化为如seqidno:105-108所示。抗体的特异性识别和结合能力主要由cdr区序列决定,fr可根据物种来设计,这是本领域公知的。例如,可设计人源、鼠源或骆驼源的fr区序列来连接上述cdr,从而得到一个可结合人pd1的多肽或结构域。
在一个优选实施方案中,所述多肽为单克隆抗体。
在一个优选实施方案中,所述多肽为vhh。
在一个优选实施方案中,所述多肽为骆驼源的vhh或人源化的vhh。
在一个具体实施方案中,所述多肽的cdr序列如下:cdr1的序列为seqidno:1,cdr2的序列为seqidno:35,并且cdr3的序列为seqidno:64。
在一个具体实施方案中,所述多肽的cdr序列如下:
i)cdr1的序列选自seqidno:9-11;并且
ii)cdr2的序列为39或43;并且
iii)cdr3的序列选自seqidno:72-74。
优选地,cdr1的序列为seqidno:9,cdr2的序列为seqidno:39,并且cdr3的序列为seqidno:72;或
cdr1的序列为seqidno:10,cdr2的序列为seqidno:39,并且cdr3的序列为seqidno:73;或
cdr1的序列为seqidno:11,cdr2的序列为seqidno:43,并且cdr3的序列为seqidno:74。
在一个具体实施方案中,所述多肽的cdr序列如下:
i)cdr1的序列为seqidno:13、14或33;并且
ii)cdr2的序列为45;并且
iii)cdr3的序列为seqidno:76或77。
优选地,cdr1的序列为seqidno:13,cdr2的序列为seqidno:45,并且cdr3的序列为seqidno:76;或
cdr1的序列为seqidno:14,cdr2的序列为seqidno:45,并且cdr3的序列为seqidno:77;或
cdr1的序列为seqidno:33,cdr2的序列为seqidno:45,并且cdr3的序列为seqidno:77。
在一个具体实施方案中,所述多肽的cdr序列如下:
i)cdr1的序列为seqidno:17;并且
ii)cdr2的序列为48或49;并且
iii)cdr3的序列选自seqidno:80-82。
优选地,cdr1的序列为seqidno:17,cdr2的序列为seqidno:48,并且cdr3的序列为seqidno:80;或
cdr1的序列为seqidno:17,cdr2的序列为seqidno:48,并且cdr3的序列为seqidno:82;或
cdr1的序列为seqidno:17,cdr2的序列为seqidno:49,并且cdr3的序列为seqidno:81。
在一个具体实施方案中,所述多肽的cdr序列如下:
i)cdr1的序列选自seqidno:19-26;并且
ii)cdr2的序列选自51-56;并且
iii)cdr3的序列选自seqidno:84-93。
优选地,cdr1的序列为seqidno:19,cdr2的序列为seqidno:51,并且cdr3的序列为seqidno:84;或
cdr1的序列为seqidno:20,cdr2的序列为seqidno:52,并且cdr3的序列为seqidno:85;或
cdr1的序列为seqidno:21,cdr2的序列为seqidno:53,并且cdr3的序列为seqidno:86;或
cdr1的序列为seqidno:22,cdr2的序列为seqidno:54,并且cdr3的序列为seqidno:87;或
cdr1的序列为seqidno:23,cdr2的序列为seqidno:55,并且cdr3的序列为seqidno:88;或
cdr1的序列为seqidno:26,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:93;或
cdr1的序列为seqidno:25,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:91;或
cdr1的序列为seqidno:24,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:89;或
cdr1的序列为seqidno:24,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:90;或
cdr1的序列为seqidno:26,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:93;或
cdr1的序列为seqidno:25,cdr2的序列为seqidno:56,并且cdr3的序列为seqidno:92。
本发明针对高表达pd-l1的肿瘤或传染病患者进行纳米抗体药物开发,通过制备pd-l1蛋白、免疫骆驼、利用噬菌体库展示纳米单抗的平台技术等,筛选到特异性结合pd-l1的纳米抗体vhh,鉴定了其cdr序列。本发明为高表达pdl1的肿瘤患者或传染病患者提供潜在的纳米抗体新药。
附图说明
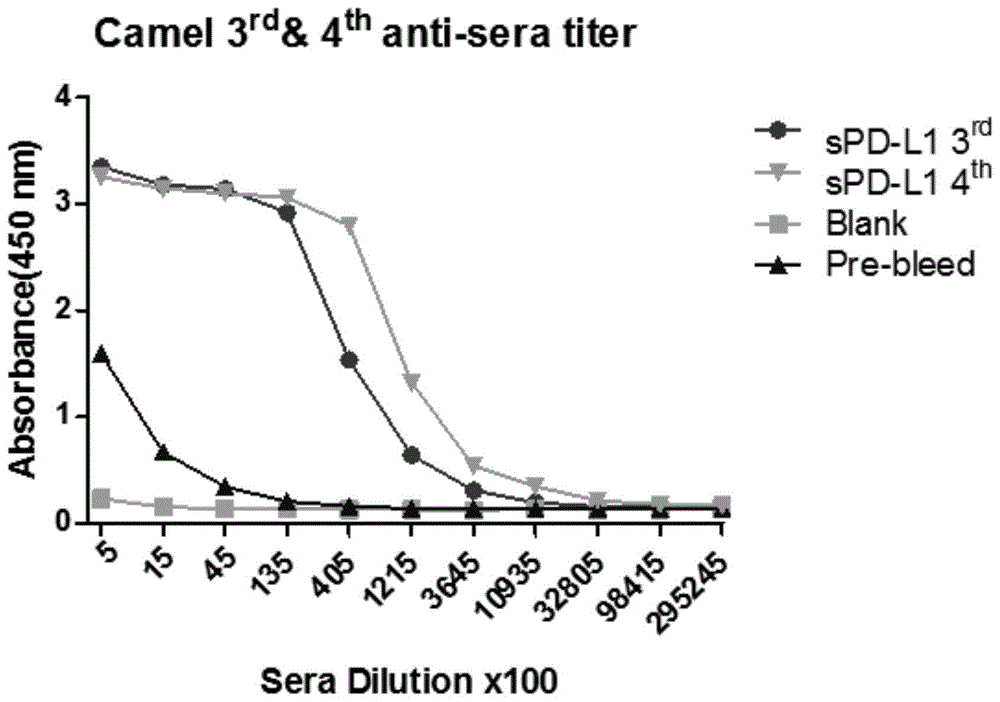
图1为pd-l1第3和4次免疫骆驼一周后的抗血清效价检测曲线;
图2为不同稀释度的第3次和第4次免疫骆驼一周后的抗血清结合pd-l1蛋白的曲线,以免疫前的血清为对照;
图3为spdl1-vhh噬菌体抗体文库为模板扩增的pcr产物的电泳图;
图4为spdl1-vhh噬菌体抗体文库的淘选鉴定,其中,a为噬菌体文库针对spd-l1蛋白淘选后elisa检测统计图;b为从第二轮(2nd)和第三轮(3rd)淘选后的噬菌体抗体文库分别挑选40个和46个克隆进行噬菌体elisa检测统计图;
图5为原核表达的vhh抗体的elisa检测统计图,每个点代表一个克隆,纵坐标为针对spd-l1的od450/空白对照的od450,比值大于5.0定义为阳性。
图6为175个细菌上清与spd-l1结合的读值和与空白对照的读值的比值。
具体实施方式
1.免疫原的制备
我们依据ncbi网站上的pd-l1蛋白序列和基因序列信息,分析并设计了可有效诱导骆驼产生针对pd-l1蛋白的特异性抗体的多肽spdl1,在c端连接his-tag(spd-l1-his)或兔fc(spd-l1-rfc)用于后续纯化及检测。
2.骆驼免疫与抗血清的获得
用250μgspd-l1-rfc蛋白与250μl弗氏完全佐剂的乳化混合物对双峰骆驼进行初免,在第14天、28天、42天用spd-l1-rfc蛋白与250μl弗氏不完全佐剂加强免疫3次,第2次和第3次免疫1周后,采血检测抗血清滴度;第4次免疫1周后,采血200ml用于噬菌体抗体库的构建。
抗血清效价通过elisa检测,用浓度为0.5μg/ml的pd-l1蛋白包被检测板,每孔加入梯度稀释的抗血清或者纯化的抗体100μl(对照为免疫前骆驼血清),37℃孵育1.5h,洗涤2次,每孔加入1:10000稀释的辣根过氧化物酶标记的goatanti-llammaigg(h+l)二抗,37℃孵育1h,洗涤4-6次后,加100μltmb底物,37℃孵育10min,50μl0.2m的h2so4中止反应,测定od450nm。elisa检测血清效价规定为在od450是空白对照的2.1倍以上并且大于0.2的最高稀释倍数。
结果如图1所示,3免和4免的抗血清效价分别为3.65×105和1.09×106。由此可见,该抗原可诱导骆驼产生特异性针对pd-l1蛋白的高滴度抗血清。
3.vhh噬菌体库构建及淘选
收集200ml免疫后骆驼的外周血,利用淋巴细胞分离液(geficoll-paqueplus)分离获得骆驼的pbmc,根据trizol操作手册,提取rna,并利用oligo(dt)反转为cdna,通过引物扩增,以及分子克隆等技术,将骆驼的vhh基因克隆至phagemid质粒,转化tg1细菌,得到vhh噬菌体库。为了进一步鉴定sgn-vhh噬菌体库是否构建成功,通过pcr扩增免疫spd-l1骆驼的vhh目的基因,可以看出目的条带为500bp,大小符合预期(图3),说明该spd-l1-vhh噬菌体抗体文库里含有vhh基因。挑选39个克隆进行测序,测序结果显示,所测序列没有完全一致的重复序列;比对结果显示,差异序列大多在cdr结合区。经检测,该构建了一个spd-l1-vhh噬菌体抗体文库的库容为1.0×109,阳性率为97.8%,序列多样性(diversity)为100%,有效插入率(inframerate)大于92%。
在m13ko7辅助噬菌体的帮助下,用vhh-phagemid转化的细菌,进行噬菌体抗体库的复苏,并用peg/nacl进行沉淀。将包被有50μg/ml的spd-l1-his蛋白进行三次富集噬菌体抗体库。将富集的噬菌体,洗脱、转化、涂板、挑取单克隆进行噬菌体与spd-l1蛋白elisa的结合鉴定,将结合读值>1.0的克隆进行测序,并克隆至表达载体pvax1,转染293f细胞表达生产纳米单抗。
淘选后的文库与pd-l1蛋白进行结合检测。噬菌体elisa结果显示,没有富集前的spd-l1-vhh噬菌体文库与spd-l1蛋白的结合读值为3.40,经过一轮、二轮、三轮富集后的噬菌体文库读值分别为1.66、7.57、12.84(图4)。为了进一步验证富集后的文库中结合spd-l1-vhh蛋白的阳性噬菌体率,从第2轮和第3轮富集后的文库里各挑选了40个克隆进行单个噬菌体elisa检测。结果显示,第2轮文库里,12.5%的单个噬菌体克隆为阳性,第3轮文库里21.1%的噬菌体克隆克隆为阳性,而且结合的读值/空白对照的读值大于3.0(图5),通过spd-l1蛋白淘选成功的富集了高结合力的spd-l1-vhh噬菌体文库。
4.vhh原核表达文库的构建及vhh表达
对上述二轮和三轮淘选富集后的2nd-sgn-vhh和3rd-sgn-vhh噬菌体抗体文库进行pcr扩增;获取并纯化抗体库中所有vhh的基因片段,将vhh的基因片段克隆至原核表达载体,转化ss320菌株,构建vhh的原核表达抗体库;将原核表达抗体库涂布平板,过夜培养,次日随机挑选单克隆菌落1000个,使用iptg诱导表达抗体上清,对抗体上清与spd-l1蛋白进行elisa结合检测。
结果显示,有175个细菌上清与spd-l1蛋白结合,同时不与空白对照结合,spd-l1结合的读值/空白对照的读值大于5.0(图6和表1)。将175个序列进行测序比对,剔除重复序列,最终获得91个的vhh抗体序列。进一步的实验证实,这91个vhh抗体以及从vhh抗体得到的cdr均可特异性地结合pd-l1蛋白。
表191个vhh抗体与spd-l1蛋白的结合值及其序列
5.流式细胞法检测vhh抗体阻断pdl1与t细胞的结合
将vhh抗体、pdl1与h9细胞(t淋巴细胞系)混合孵育,100μl/样品,4℃1h;以0.5%pbsf洗涤两遍后,加入二抗alexafluor488goatantihumanigg,4℃30min;以0.5%pbsf洗涤两遍后,上机检测。结果显示,上述pdl1被抗体中和,不能结合到h9细胞上。使用人源化的vhh抗体亦得到类似的结果。可见,上述vhh抗体具有中和pdl1的能力,使其无法与t细胞表面的pd1分子结合,避免表达pdl1的肿瘤逃避免疫机制,从而达到治疗或者抑制肿瘤生长的效果,因此这些vhh抗体均有潜力成为治疗肿瘤的新型抗体药物。由于上述vhh抗体具有中和pdl1的能力,同时有可能通过阻断pdl1激活pd1的机会,从而通过增强t淋巴细胞杀伤病毒或者细菌的能力,最终达到防控传染病的目的,因此这些vhh抗体均有潜力成为治疗传染病的新型抗体药物。
6.使用aav病毒载体装载的人源化vhh进行体内实验
腺相关病毒载体(aav)源于非致病的野生型腺相关病毒,由于其安全性好、宿主细胞范围广(分裂和非分裂细胞)、免疫源性低,在体内表达外源基因时间长等特点,被视为最有前途的基因转移载体之一,在世界范围内的基因治疗和疫苗研究中得到广泛应用。
aavhelper-free病毒包装系统购于cellbiolabs,sandiegousa。将上述vhh的dna编码序列通过分子克隆技术插入到paav-mcs质粒;通过测序证明构建成功后,将构建好的质粒paav-ab与phelper和paav-dj质粒按照质量比1:1:1的方式使用pei转染试剂共转染aav-293t细胞。转染后分别于48、72、96和120小时收集上清,并用5xpeg8000(sigma)进行浓缩,最后用1.37g/ml氯化铯进行纯化。纯化的aav溶解于pbs里,进行鉴定和分装后保存于-80℃。
将aav-vhh注射至pdl1阳性的小鼠肿瘤,结果显示aav-vhh对肿瘤有良好的治疗效果。
以上所述仅为本发明的较佳实施例,并不用以限制本发明,凡在本发明的精神和原则之内,所作的任何修改、等同替换、改进等,均应包含在本发明的保护范围之内。
序列表
<110>源道隆(苏州)医学科技有限公司
<120>可结合pd-l1的多肽及其应用
<160>108
<170>siposequencelisting1.0
<210>1
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>1
gluserileargasnvalhisile
15
<210>2
<211>5
<212>prt
<213>人工序列(artificialsequence)
<400>2
pheaspmetargthr
15
<210>3
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>3
glyalaasppheasnpheasnser
15
<210>4
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>4
glyaspserilethrthralaglytyrser
1510
<210>5
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>5
glyglualailethralalystyrsertyr
1510
<210>6
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>6
glyphethrpheserserasntrp
15
<210>7
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>7
glyphethrpheserthrtyrala
15
<210>8
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>8
glyphethrleuaspargtyrthr
15
<210>9
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>9
glyglyserilethrthrasntyrtyrphe
1510
<210>10
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>10
glyglyserilethrthrasntyrtyrtyr
1510
<210>11
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>11
glyglyservalalathrasntyrtyrtyr
1510
<210>12
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>12
glyglythrpheargphetyrthr
15
<210>13
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>13
glyglythrvalasnasntyrtyr
15
<210>14
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>14
glyhisthrvalasnasntyrala
15
<210>15
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>15
glyileasnleuasphishisval
15
<210>16
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>16
glyleuvalpheserseralapro
15
<210>17
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>17
glyargalapheleuthrtyrser
15
<210>18
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>18
glyargmetpheargileasnthr
15
<210>19
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>19
glyargthrpheilesertyrala
15
<210>20
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>20
glyargthrpheasnglntyrthr
15
<210>21
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>21
glyargthrpheargsertyrala
15
<210>22
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>22
glyargthrpheserlystyrala
15
<210>23
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>23
glyargthrpheserprotyrala
15
<210>24
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>24
glyargthrpheserthrleuhis
15
<210>25
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>25
glyargthrpheserthrserhis
15
<210>26
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>26
glyargthrphesertyrphehis
15
<210>27
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>27
glyargthrphethrsertyrala
15
<210>28
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>28
glyserileargargilehisser
15
<210>29
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>29
glyserserserargilethrglu
15
<210>30
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>30
glyserthrphesersersertrp
15
<210>31
<211>6
<212>prt
<213>人工序列(artificialsequence)
<400>31
ilepheaspsertyrala
15
<210>32
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>32
ileargthrphethrmetthrser
15
<210>33
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>33
argargleuasptyrtyrala
15
<210>34
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>34
servalthrserserileasnthr
15
<210>35
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>35
ileilealaasnglyasnthr
15
<210>36
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>36
ilesertrpasnglyileserser
15
<210>37
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>37
valthralaglyaspargthr
15
<210>38
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>38
ilesertyrserglyhisser
15
<210>39
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>39
ilealatyrserglyserthr
15
<210>40
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>40
ileasnthraspglyaspasnser
15
<210>41
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>41
ileasnserglyglyglyserthr
15
<210>42
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>42
ileargserglyglypheala
15
<210>43
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>43
ilethraspserglyserval
15
<210>44
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>44
ileargtrpasnaspasnthrglu
15
<210>45
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>45
ilesertrpserglyglythrthr
15
<210>46
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>46
pheglytyrthrgluserlysglu
15
<210>47
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>47
ileserileglnglyvalpro
15
<210>48
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>48
valasntrpserglyserserthr
15
<210>49
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>49
glyasntrpserglythrthrthr
15
<210>50
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>50
ileserserglyglythrthr
15
<210>51
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>51
ilesertrpserglyserserthr
15
<210>52
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>52
ilesertrpargglyglyserthr
15
<210>53
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>53
ileserargserglyvalthrthr
15
<210>54
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>54
ilesertrpserglyglyserthr
15
<210>55
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>55
ilesermetasnglyglythrthr
15
<210>56
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>56
ileserargleuglyglylysthr
15
<210>57
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>57
valserglyserglyalaarglys
15
<210>58
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>58
metthrargaspglyserthr
15
<210>59
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>59
thrileileglyglyserthr
15
<210>60
<211>6
<212>prt
<213>人工序列(artificialsequence)
<400>60
ilehisthrglyalathr
15
<210>61
<211>7
<212>prt
<213>人工序列(artificialsequence)
<400>61
ilethrlysglyglylysthr
15
<210>62
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>62
ilesertrptyrproglyargthr
15
<210>63
<211>8
<212>prt
<213>人工序列(artificialsequence)
<400>63
thrleuthralavalglyilethr
15
<210>64
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>64
argalaaspvalproglytyrglyargile
1510
<210>65
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>65
alavalglnalaglnleuargglyprovalasnasptyrtyrthrarg
151015
alatyrargtyr
20
<210>66
<211>12
<212>prt
<213>人工序列(artificialsequence)
<400>66
asnvalvalvalglyhistrpileaspvalglutyr
1510
<210>67
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>67
alaalaileasnaspphehispheserser
1510
<210>68
<211>12
<212>prt
<213>人工序列(artificialsequence)
<400>68
alaargtyrserasptyralatyrglutyrasptyr
1510
<210>69
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>69
alathrhisasnalatyrargtyrglutyr
1510
<210>70
<211>15
<212>prt
<213>人工序列(artificialsequence)
<400>70
alalyscysglysertrptyralaaspasntyrglymetasptyr
151015
<210>71
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>71
alaargglythrasnaspleucystrpargglyserserasntyrasn
151015
tyr
<210>72
<211>12
<212>prt
<213>人工序列(artificialsequence)
<400>72
thrserthrthrglutrptyrprothralathrser
1510
<210>73
<211>11
<212>prt
<213>人工序列(artificialsequence)
<400>73
alaarggluglysertrppromettyrasptyr
1510
<210>74
<211>14
<212>prt
<213>人工序列(artificialsequence)
<400>74
alaargvalmetseralatrptyraspproargmetaspser
1510
<210>75
<211>19
<212>prt
<213>人工序列(artificialsequence)
<400>75
alaalaglyserargtrppropheargserlystrpargthrserasp
151015
pheserser
<210>76
<211>24
<212>prt
<213>人工序列(artificialsequence)
<400>76
alaalaasnglyprometthrmetalaserasnargasntyrvalphe
151015
thraspargasnargtyralaile
20
<210>77
<211>24
<212>prt
<213>人工序列(artificialsequence)
<400>77
alaalaasnglyprometthrmetalapheasnargasntyrvalphe
151015
seraspargasnargtyralaphe
20
<210>78
<211>18
<212>prt
<213>人工序列(artificialsequence)
<400>78
alaalaasparggluglycysleuserilealaleuvalargalatyr
151015
asptyr
<210>79
<211>5
<212>prt
<213>人工序列(artificialsequence)
<400>79
asnthrasnglntyr
15
<210>80
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>80
alaalaargleuglyalathrtrpserargargproalaasppheasp
151015
ser
<210>81
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>81
alaalaargleuglyalathrtrpserargargprocysasppheasp
151015
ser
<210>82
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>82
alaalaargleuglyalathrtrpserargargproalaaspleuasp
151015
ser
<210>83
<211>16
<212>prt
<213>人工序列(artificialsequence)
<400>83
asnalaglyalaservalargglyservalthrglytyrilegluval
151015
<210>84
<211>22
<212>prt
<213>人工序列(artificialsequence)
<400>84
alaglyargleuthralaalahisalametaspilemetthrasplys
151015
alaasnglymetasptyr
20
<210>85
<211>22
<212>prt
<213>人工序列(artificialsequence)
<400>85
alaalagluthrglnsertyrprosersersertyriletyrthrala
151015
serthrargtyrasntyr
20
<210>86
<211>14
<212>prt
<213>人工序列(artificialsequence)
<400>86
alaalaglymettyrglythrglntrpaspglutyrsertyr
1510
<210>87
<211>12
<212>prt
<213>人工序列(artificialsequence)
<400>87
alaalaasnleutyrglyleuglysertyrasptyr
1510
<210>88
<211>16
<212>prt
<213>人工序列(artificialsequence)
<400>88
alaalaargargtrpglythrsermetileserserglutyrleutyr
151015
<210>89
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>89
alavalaspproserserleualatrpvalileargthrthrprohis
151015
asptyrserasn
20
<210>90
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>90
alavalaspproserserleualatrpvalleuargthrthrprohis
151015
asptyrserasn
20
<210>91
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>91
alaalaaspproserserleualatrpvalileargserthrprohis
151015
asptyrserasn
20
<210>92
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>92
alathraspproserserleualatrpvalileargserthrprohis
151015
asptyrserasn
20
<210>93
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>93
alavalaspproserserleualatrpvalvalargthrthrprohis
151015
asptyrserasn
20
<210>94
<211>22
<212>prt
<213>人工序列(artificialsequence)
<400>94
alaalaaspserglyilethrpheserproarglysglyproproarg
151015
prothrasppheglyser
20
<210>95
<211>14
<212>prt
<213>人工序列(artificialsequence)
<400>95
asnalavalglyserserglnpheglyargleuvalglutyr
1510
<210>96
<211>9
<212>prt
<213>人工序列(artificialsequence)
<400>96
asnvalargthrleuleuargasntyr
15
<210>97
<211>9
<212>prt
<213>人工序列(artificialsequence)
<400>97
alaargglutyrleuglypheasptyr
15
<210>98
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>98
asnalaalaproglutrptrptyrglyvalproalaaspglutyrasp
151015
tyr
<210>99
<211>15
<212>prt
<213>人工序列(artificialsequence)
<400>99
alaalaaspproargglyvalileasnalatyrasptyrasntyr
151015
<210>100
<211>15
<212>prt
<213>人工序列(artificialsequence)
<400>100
tyralaargglyvalhisleuvalthrargalaleuasnasptyr
151015
<210>101
<211>25
<212>prt
<213>人工序列(artificialsequence)
<400>101
glnleuglnleuvalgluserglyglyglyleuvalglnalaglyasp
151015
serleuargleusercysalaalaser
2025
<210>102
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>102
metglytrppheargglnalaproglylysgluarggluphevalala
151015
gly
<210>103
<211>38
<212>prt
<213>人工序列(artificialsequence)
<400>103
sertyrthraspseralalysaspargphethrileserlysaspasn
151015
thrlysasnthrvaltyrleuglnmetasnserleulysprogluasp
202530
thralavaltyrleucys
35
<210>104
<211>11
<212>prt
<213>人工序列(artificialsequence)
<400>104
trpglyglnglythrglnvalthrvalserser
1510
<210>105
<211>25
<212>prt
<213>人工序列(artificialsequence)
<400>105
glnvalargleuvalgluserglyglyglyservalglnalaglyglu
151015
thrleuargleusercysthralaser
2025
<210>106
<211>17
<212>prt
<213>人工序列(artificialsequence)
<400>106
metglytrptyrargglnglyproglyasnglucysglumetvalala
151015
tyr
<210>107
<211>36
<212>prt
<213>人工序列(artificialsequence)
<400>107
alaaspserthrlysglyargphethrileserglnaspasnalalys
151015
histhrleutyrleuglnmetasnserleulysprogluaspthrgly
202530
valtyrtyrcys
35
<210>108
<211>10
<212>prt
<213>人工序列(artificialsequence)
<400>108
glyglnglythrargvalthrvalserser
1510
- 还没有人留言评论。精彩留言会获得点赞!