用于生产大麻素和其它异戊二烯化的化合物的生物合成平台
相关申请的交叉引用
本申请要求2018年8月1日提交的美国临时申请系列号62/713,348的优先权,其公开内容通过引用整体并入本文。
关于联邦资助的研究的声明
本发明在美国能源部颁布的授予号de-fc02-02er63421和国立卫生研究院颁布的授予号gm008496下在政府支持下完成。政府具有本发明的某些权利。
序列表
本申请含有序列表,其已经以ascii格式电子地提交,且特此通过引用整体并入。于2019年8月1日创建的所述ascii副本命名为sequence_st25.txt,且是287,021字节大小。
提供了通过使合适的底物与本公开内容的代谢修饰的微生物或酶促制剂接触来生产大麻素和其它异戊二烯化的化学物质和化合物的方法。
背景
天然化合物的异戊二烯化增加结构多样性,改变生物活性,并增强治疗潜力。异戊二烯化的化合物经常具有低天然丰度或难以分离。一些异戊二烯化的天然产物包括一大类具有经证实的医学特性的生物活性分子。实例包括异戊二烯基-黄酮类化合物、异戊二烯基-芪类化合物和大麻素。
大麻素是一大类具有生物活性的植物衍生的天然产物,它们调节人内源性大麻素系统的大麻素受体(cb1和cb2)。大麻素是有前途的药理学试剂,目前正在进行100多项研究其作为止吐药、抗惊厥药、镇痛药和抗抑郁药的治疗益处的临床试验。进一步,三种大麻素疗法已被fda批准用于治疗化学疗法引起的恶心、ms痉挛状态和与严重癫痫相关的癫痫发作。
尽管它们具有治疗潜力,但药用级(>99%)大麻素的生产仍然面临重大技术挑战。印度大麻脂(cannibis)植物如食用性大麻(marijuana)和工业大麻(hemp)产生高水平的四氢大麻酚酸(thca)和大麻二酚酸(cbda),以及多种较低丰度的大麻素。但是,由于污染性大麻素的高度结构相似性以及每种作物的大麻素组成的变化,即使高度表达的大麻素(如cbda和thca)的分离也是有挑战性的。当尝试分离稀有大麻素时,这些问题被放大。此外,当前的印度大麻(cannabis)种植实践带来了严重的环境挑战。结果,对开发用于生产大麻素和大麻素类似物的替代方法存在相当大的兴趣。
技术实现要素:
本公开内容提供了一种重组多肽,其包含选自以下的序列:(a)seqidno:30且具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸;(b)seqidno:30,其具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸,和至少一个选自v49z1、f213z2、a232s、i234t、v271z3和/或g286s的其它突变,其中z1是s、n、t或g,z2是h、n或g且z3是n或h;(c)在表1中所示的突变组合中的任一种;(d)(a)、(b)或(c)中的任一种,其包含1-20个保守氨基酸置换且具有nphb异戊二烯基转移酶活性;(e)与seqidno:30具有至少85%、90%、95%、98%或99%同一性且至少具有在(a)、(b)或(c)中列举的突变的序列;(f)从氨基酸21开始在seqidno:1-28或29中列举的序列;和(g)与seqidno:1-28或29中的任一个具有至少99%同一性的任何序列,其中(a)-(g)中的任一项的多肽执行异戊二烯化反应。在一个实施方案中,所述异戊二烯化反应包括从gpp和油橄榄醇酯(olivetolate)产生cbga,或从gpp和divarinicacid产生cbgva,或从2,4-二羟基苯甲酸或其在c6位置具有化学基团的衍生物(参见,例如,式i)产生cbgxa。
式i
其中‘x’可以是卤素、羟基、氰基、硝基、酯、烷氧基、氨基、巯基、亚磺酰基、磺酰基、亚磺基、磺基、硫氰酰基、异硫氰酰基、硫醛、二羟硼基、硼酸酯、磷酸酯、醛、羧基、羧酰氨基、叠氮基、氰酰、异氰酰、任选地被取代的(c1-c10)烷基、任选地被取代的(c2-c10)烯基、任选地被取代的(c2-c10)炔基、任选地被取代的(c1-c10)杂烷基、任选地被取代的(c2-c10)杂烯基、任选地被取代的(c2-c10)杂炔基、任选地被取代的(c3-c10)环烷基、任选地被取代的芳基和任选地被取代的杂环。在一个实施方案中,x是被取代的或未被取代的含有2-10个碳的烷基。
本公开内容也提供了包含多肽的重组途径,所述多肽具有选自以下的序列:(a)seqidno:30且具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸;(b)seqidno:30,其具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸,和至少一个选自v49z1、f213z2、a232s、i234t、v271z3和/或g286s的其它突变,其中z1是s、n、t或g,z2是h、n或g且z3是n或h;(c)在表1中所示的突变组合中的任一种;(d)(i)、(ii)或(iii)中的任一种,其包含1-20个保守氨基酸置换且具有nphb活性;(e)与seqidno:30具有至少85%、90%、95%、98%或99%同一性且至少具有在(i)、(ii)或(iii)中列举的突变的序列;(f)从氨基酸21开始在seqidno:1-28或29中列举的序列;和(g)与seqidno:1-28或29中的任一个具有至少99%同一性的任何序列,和多种将葡萄糖转化为香叶基焦磷酸酯的酶;和(h)与seqidno:1-28或29中的任一个具有至少99%同一性的任何序列,和多种将(异)戊二烯醇转化为香叶基焦磷酸酯的酶。在另一个实施方案中,所述方法还包括丙酮酸脱氢酶旁路酶途径,其包含丙酮酸氧化酶和乙酰基磷酸转移酶。在另一个或其它实施方案中,所述途径包含再循环nadh/nad和nadph/nadp的“净化阀”。在前述任一个的另一个或其它实施方案中,所述途径包含以下酶:(i)己糖激酶(hex);(ii)葡萄糖-6-磷酸异构酶(pgi);(iii)磷酸果糖激酶(pfk);(iv)果糖-1,6-二磷酸醛缩酶(fba);(v)磷酸丙糖异构酶(tpi);(vi)gald-3-p脱氢酶(gap);(vii)突变体gald-3-p脱氢酶(mgap);(viii)nadh氧化酶(nox);(ix)磷酸甘油酸激酶(pgk);(x)磷酸甘油酸酯变位酶(2,3bpg依赖性的)(dpgm);(xi)烯醇化酶(eno);(xii)丙酮酸激酶(fbp依赖性的);(xiii)丙酮酸氧化酶(pyox);(xiv)乙酰基磷酸转移酶(pta);(xv)乙酰辅酶a乙酰基转移酶(phaa);(xvi)hmg-coa合酶(hmgs);(xvii)hmg-coa还原酶(hmgr);(xviii)甲羟戊酸激酶(mvk);(xix)磷酸甲羟戊酸激酶(pmvk);(xx)二磷酸甲羟戊酸脱羧酶(mdc);(xxi)异戊烯基二磷酸异构酶(idi);(xxii)香叶基-pp合酶(gpps);和;(xxiii)突变体芳族异戊二烯基转移酶。在任一个前述实施方案的另一个实施方案中,除了磷酸甲羟戊酸脱羧酶(pmdc)和异戊烯基-磷酸激酶(ipk)以外,所述途径包含上面的酶(i)至(xviii)和(xxii)至(xxiii)。在另一个或其它实施方案中,所述途径包含4-步骤途径以使用atp和一个或多个再循环adp/atp的步骤将异戊二烯醇或戊二烯醇转化为gpp。在前述任一个的另一个或其它实施方案中,所述途径包含(a)(异)戊二烯醇激酶(prk);(b)异戊烯基磷酸激酶(ipk);(c)异戊烯基二磷酸异构酶(idi);和(d)香叶基焦磷酸酯合酶(gpps)。在再一个或其它实施方案中,给所述途径补充atp和油橄榄醇酯(或2,4-二羟基苯甲酸或其衍生物)且所述途径产生大麻素前体。在另一个实施方案中,所述途径进一步包含大麻二酚酸合酶。在再一个或其它实施方案中,所述途径产生大麻二酚酸。
本公开内容也提供了一种生产异戊二烯化的化合物的方法,所述方法包括在有重组多肽存在下使底物与具有以下通用结构的异戊二烯基接触:
所述重组多肽具有选自以下的序列:(a)seqidno:30且具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸;(b)seqidno:30,其具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸,和至少一个选自v49z1、f213z2、a232s、i234t、v271z3和/或g286s的其它突变,其中z1是s、n、t或g,z2是h、n或g且z3是n或h;(c)在表1中所示的突变组合中的任一种;(d)(i)、(ii)或(iii)中的任一种,其包含1-20个保守氨基酸置换且具有nphb活性;(e)与seqidno:30具有至少85%、90%、95%、98%或99%同一性且至少具有在(i)、(ii)或(iii)中列举的突变的序列;(f)从氨基酸21开始在seqidno:1-28或29中列举的序列;和(g)与seqidno:1-28或29中的任一个具有至少99%同一性的任何序列,其中所述异戊二烯基添加至所述底物。
在附图和以下描述中阐述了本公开内容的一个或多个实施方案的细节。从说明书和附图以及从权利要求书会明白其它特征、目的和优点。
附图简要说明
并入本说明书中并构成本说明书的一部分的附图说明了本公开内容的一个或多个实施方案,并且与详细描述一起用于解释本发明的原理和实施方式。
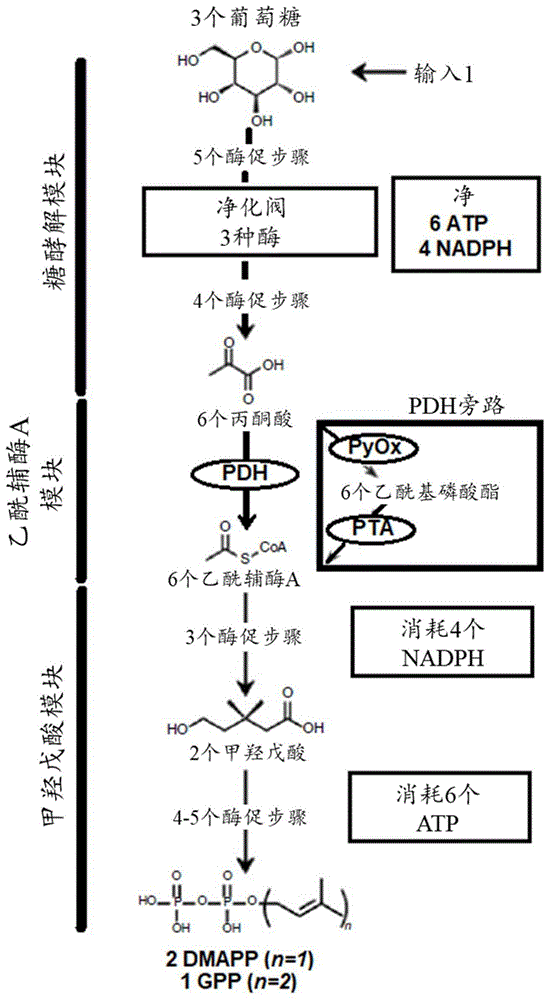
图1a-b描绘了本公开内容的示例性生物合成途径。(a)用于产生异戊二烯基天然产物的生物化学合成平台.首先,通过经修饰以调节nadph水平的糖酵解途径将葡萄糖分解为丙酮酸(12个酶促步骤)。然后,pdh或pdh旁路将丙酮酸转化为乙酰辅酶a。乙酰辅酶a通过甲羟戊酸途径转化为gpp(8个酶促步骤)。通过改变芳族异戊二烯基转移酶(apt)和芳族底物,可以使用相同的中心途径产生多种异戊二烯基-类黄酮和异戊二烯基-芪类化合物。开发了异戊二烯基转移酶nphb的变体(dnphb)以生产cbga或cbgva。通过大麻二酚酸合酶(cbdas),cbga转化为大麻二酚酸(cbda)且cbgva转化为次大麻二酚酸(cbdva)。通过使用不同的大麻素合酶(thcas和cbcas)可能生产其它大麻素。(b)描绘了(a)的途径的更详细视图。葡萄糖通过糖酵解分解为丙酮酸(深蓝色)。以深蓝色描绘的净化阀允许碳通量继续通过糖酵解途径,而不会积累过量的nadph。丙酮酸通过以浅蓝色描绘的pdh旁路转化为乙酰辅酶a。乙酰辅酶a通过甲羟戊酸途径(水)积累在高能磷酸酯分子中以产生gpp。然后,来自甲羟戊酸途径的gpp被用于对芳族聚酮化合物进行异戊二烯化。此处显示了油橄榄醇酯的异戊二烯化以产生cbga;但是,油橄榄醇酯可以用多种底物(芳族和非芳族)代替以生成各种异戊二烯化的产物。最后,使用cbdas将cbga转化为cbda。自发脱羧完成向cbda的生物合成途径。cbda的生产完成了以绿色显示的大麻素模块。
图2a-d显示了用于异戊二烯化芳族聚酮化合物的pdh旁路的发展。(a)在各种芳族聚酮化合物和2%乙醇(媒介物)的存在下测量丙酮酸脱氢酶(ecpdh)的活性(n=3)。(b)使用pdh(pdh系统-灰色迹线)和pdh旁路系统(蓝色迹线)在不同浓度的1,6dhn下通过完整途径实现的最终滴度的对比。误差条代表样品之间的标准偏差(n=3)。(c)使用wtnphb用pdh旁路系统随时间产生的5-异戊二烯基-1,6-dhn蓝色迹线和cbga绿色迹线的量。误差条代表样品之间的标准偏差(n=3)。(d)使用nphb、atapt或novq异戊二烯基转移酶将各种芳族底物添加至所述途径(生物学重复,n=3)。结果是各种c5和c10异戊二烯基-天然产物(*指示未确定滴度)。
图3a-c显示了nphb的工程改造以改善cbga生产。(a)wtnphb的活性位点中的油橄榄醇酯的模型。在设计过程期间,允许残基a288、g286和a232和i234、v271和v49发生变化。残基a288、g286和a232对关于oa的活性具有最大影响,并且是在聚焦文库中靶向的位置。(b)活性测定的结果,以确定以油橄榄醇酯为底物的nphb突变体的近似活性。倍数提高是用gpp(2.5mm)、油橄榄醇酯(5mm)、mgcl2(5mm)和1mg/mlwtnphb和突变体进行三次重复反应的平均值。(c)与cbga标准品相比使用m23和wtnphb的完整途径反应产物的gc-ms色谱图。m23突变体显著提高了对于正确产物的特异性。
图4a-c显示了用于生产各种大麻素的无细胞异戊二烯化系统的评价。(a)随着时间的流逝,大麻素前体的无细胞酶促生产(从葡萄糖)。使用m23的cbga生产显示为浅绿色迹线,且wtnphb显示为深绿色迹线。使用m31的cbgva生产显示为浅蓝色迹线。用于wt、m23和m31的nphb的浓度固定在0.5mg/ml(n=3)。(b)使用壬烷流cbga捕获系统,获得更高的cbga滴度(1.2g/l)。使用蠕动泵交换壬烷层,该蠕动泵使壬烷沿箭头所示方向循环。该系统能够将cbga稀释进数毫升的壬烷和缓冲液中,这减少反应中cbga的量。(c)使用cbdas随时间推移生产大麻素。cbda生产显示为深紫色迹线,且cbdva生产显示为浅紫色迹线。
图5a-c显示了matb和mdca(转移酶)路径的途径示意图。(a)这是matb路径的示意图。丙二酰基辅酶a生产是atp依赖性的,但是在其它方面与途径无关。所述途径的滴度为12mg/l。(b)这是mdca转移酶路径的示意图。丙二酰基辅酶a生产不再是atp依赖性的,而是与丙酮酸氧化路径和甲羟戊酸路径有关。该系统的滴度为42mg/l。(c)显示了在(a)和(b)中示出的途径的聚酮化合物模块中的示例性步骤的额外细节。
图6显示了(异)戊二烯醇至gpp路径的途径示意图。可以使用atp和必要的激酶将异戊二烯醇或戊二烯醇转化成香叶基焦磷酸酯。
图7显示了可用于从乙酰辅酶a(或甲羟戊酸)产生ipp/dmapp的各种规范的(真核)和非规范的(古细菌i和ii)甲羟戊酸途径。
具体实施方式
如在本文中和在所附权利要求书中所使用的,单数形式“一个/种(a)”、“一个/种(an)”和“该”包括复数指示物,除非上下文另外清楚地指明。因此,例如,对“一种多核苷酸”的提及包括多种这样的多核苷酸,且对“该酶”的提及包括对一种或多种酶的提及,诸如此类。
除非另外定义,在本文中使用的所有技术和科学术语具有与本公开内容所属领域的普通技术人员通常理解的含义相同的含义。尽管与本文描述的那些类似或等同的方法和材料可以用于所公开的方法和组合物的实践中,但是本文描述了示例性的方法、装置和材料。
并且,除非另外说明,“或”的使用是指“和/或”。类似地,“包含(comprise)”、“包含(comprises)”、“包含(comprising)”、“包括(include)”、“包括(includes)”和“包括(including)”是可互换的,并不旨在进行限制。
还应当理解,在各个实施方案的描述使用术语“包含”的情况下,本领域技术人员会理解,在一些具体情况下,可以可替换地使用语言“基本上由……组成”或“由……组成”描述一个实施方案。
在上面以及贯穿全文所讨论的任何出版物仅仅出于其在本申请的申请日之前公开的目的而提供。本文中的任何内容均不应解释为承认:发明人由于在先公开而无权领先于这样的公开。
异戊二烯化(也被称作异戊二烯基化或脂质化)是将疏水性分子添加至蛋白或化学化合物。通常假定异戊二烯基(3-甲基丁-2-烯-1-基)有助于向细胞膜附着,类似于脂质锚,如gpi锚。已显示异戊二烯基对于通过专门的异戊二烯基-结合结构域的蛋白-蛋白结合而言是重要的。
异戊二烯化的天然产物是具有经证实的医学特性的一大类生物活性分子。实例包括异戊二烯基-黄酮类化合物、异戊二烯基-芪类化合物和大麻素。由于污染性分子的结构相似性以及作物之间的可变组成,难以分离植物来源的异戊二烯化合物。当尝试分离低丰度化合物时,这些挑战会进一步加剧。已经开发了许多化学合成来解决与制备异戊二烯化的天然产物有关的挑战,但是由于复杂程度和低产率,它们对于药物制造而言通常是不切实际的。
对于异戊二烯化的天然产物,微生物生产是自然提取的有用替代方案,但是伴随着许多挑战,诸如需要将碳通量从中心代谢和产物毒性转移,仅举几个例子。例如,异戊二烯基-天然产物如异戊二烯基-柚皮素、异戊二烯基-白藜芦醇和大麻二酚酸(cbda)源自脂肪酸、类异戊二烯和聚酮化合物生物合成的代谢途径的组合。因此,高水平的生产需要有效地重新设计长的、必不可少的和高度调节的途径。尽管存在挑战,但许多研究组已经工程改造微生物来产生未异戊二烯化的聚酮化合物如柚皮素、白藜芦醇和油橄榄醇酯,但在相对低的水平(分别为110、391和80mg/l)。获得异戊二烯化的产物甚至更有挑战性,因为香叶基-焦磷酸酯(gpp)是必需的代谢产物,其在中等浓度对细胞有毒,从而为高水平微生物生产造成重要障碍。
大麻素特别显示出巨大的治疗潜力,正在进行超过100项作为止吐药、抗惊厥药、抗抑郁药和镇痛药的临床试验。尽管如此,尽管异戊二烯基-天然产物具有治疗潜力,但由于缺乏有成本效益的生产方法,其研究和应用受到限制。
基于植物的大麻素生产的两个主要替代方案是有机合成和在代谢工程改造的宿主(例如植物、酵母或细菌)中的生产。已经阐明了用于生产一些大麻素(诸如thca和cbda)的总合成,但它们通常不适用于药物制造。另外,合成方法不是模块化的,需要对每种大麻素进行独特合成。模块方案可以通过使用天然的生物合成途径来实现。
三种主要的大麻素(thca、cbda和cannibichromene或cbca)衍生自单一前体cbga。此外,从cbgva衍生出三种低丰度大麻素(图1a)。因此,在异源宿主中制备cbga和cbgva的能力将为生产一系列大麻素打开大门。不幸的是,工程改造微生物以生产cbga和cbgva已被证明极具挑战性。
大麻素衍生自脂肪酸、聚酮化合物和萜烯生物合成途径的组合,所述途径生成关键的结构单元香叶基焦磷酸酯(gpp)和油橄榄醇酸(oa)(图1a)。高水平cbga生物合成需要重新设计长的、必不可少的和高度调节的途径。此外,gpp对细胞有毒,对在微生物中的高水平生产造成明显障碍。尽管gagne等人(proc.natl.acad.sci.,109:12811,2012)工程改造了一个途径来在酵母中生产oa,但是滴度是非常低的(0.5mgl-1),从而提示,在所述途径上的中间体的高水平生产并不容易。在一项单独的研究中,zirpel等人在含有混杂的异戊二烯基转移酶(nphb)和thca合酶并补充了gpp和油橄榄醇酸(oa)的酵母裂解物中生产了thca(j.biotechnol.,259:204-212,2017)。但是,仍然没有公开的报告表明从低成本原料在经工程改造的活细胞中生产大麻素。
在合成生物化学中,使用酶的混合物无细胞地进行复杂的生物化学转化,与传统的代谢工程改造相比具有潜在的优点,包括:在途径设计中更高的灵活性水平;对组分优化的更大控制;更快的设计-建造-测试周期;和没有中间体或产物的细胞毒性。本公开内容提供了用于生产大麻素的无细胞系统。
本公开内容提供了酶变体和包含此类变体的途径,其用于化合物的异戊二烯化,包括大麻素的产生。另外,本文所述的生物合成途径使用“净化阀”来调节nad(p)h水平。这样的“净化阀”已经证实从葡萄糖高水平生产单萜,表明可以无细胞产生大量gpp(参见,国际专利公开wo2017/015429,其公开内容通过引用并入本文)。这些净化阀用于升级和多样化原始系统,以生产复杂天然产物诸如大麻素。图1a、1b、5a和5b中概述了合成生物化学方法。在一个实施方案中,本公开内容提供了一种使用衍生自葡萄糖的gpp用于异戊二烯化的无细胞系统(参见,图1a、1b、5a、5b和7)。在另一个实施方案中,本公开内容提供了一种使用衍生自(异)戊二烯醇或戊二烯醇的gpp进行异戊二烯化的无细胞系统(参见,图6)。图6的途径可以与任何atp产生系统偶联以产生反应所需的atp。例如,所述途径可以与肌酸激酶atp产生系统;乙酸激酶系统;糖酵解系统以及其它系统偶联。图6的酶(核酸编码序列和多肽)提供在seqidno:54-65中(例如,prk酶提供在seqidno:54-57中;ipk酶提供在seqidno:58-61中;idi酶提供在seqidno:62-63中;且fpps酶提供在seqidno:64-65中)。
nphb是一种芳族异戊二烯基转移酶,其催化10-碳香叶基与芳族底物的连接。nphb表现出富集底物选择性和产物区域选择性。从链霉菌属(streptomyces)鉴定出的nphb催化10-碳香叶基向许多小的有机芳族底物的添加。nphb具有一个宽敞且溶剂可接近的结合口袋,两种底物分子香叶基二磷酸酯(gpp)和1,6-二羟基萘(1,6-dhn)可以结合在该结合口袋中。除了mg2+以外,gpp通过其带负电荷的二磷酸酯部分与几个氨基酸侧链(包括lys119、thr171、arg228、tyr216和lys284)之间的相互作用而稳定。nphb的活性需要mg2+辅因子。来自链霉菌属的nphb具有如seqidno:30中所示的序列。
novq(登记号aaf67510,通过引用并入本文)是异戊二烯基转移酶的cloq/nphb类的一个成员。novq基因可以从雪白链霉菌(streptomycesniveus)克隆,其产生氨基香豆素抗生素新生霉素。重组novq可在大肠杆菌中表达并纯化至同质。纯化的酶是40-kda的可溶性单体蛋白,其独立于二价阳离子催化二甲基烯丙基向4-羟基苯基丙酮酸酯(4-hpp)的转移,以生成3-二甲基烯丙基-4-hpp,即新生霉素的中间体。除了4-hpp的异戊二烯化外,novq还催化各种苯丙素(phenylpropanoids)、类黄酮和二羟基萘的基于碳-碳的和基于碳-氧的异戊二烯化。尽管其催化混杂,但novq催化的异戊二烯化以区域特异性方式发生。novq是第一种报告的异戊二烯基转移酶,其能够催化二甲基烯丙基向苯丙素(诸如对香豆酸和咖啡酸)和类黄酮的b环的转移。novq可以充当用于合成异戊二烯化的苯丙素和异戊二烯化的类黄酮的有用生物催化剂。
最近被发现和表征的土曲霉(aspergillusterreus)芳族异戊二烯基转移酶(atapt;登记号amb20850,通过引用并入本文)负责各种芳族化合物的异戊二烯化。重组atapt可以在大肠杆菌中过表达并纯化。在有不同的异戊二烯基二磷酸酯存在下,土曲霉芳族异戊二烯基转移酶(atapt)主要催化酰基间苯三酚的c-单异戊二烯化。
油橄榄醇酸(oa)是野生型nphb的相对较差的底物。所以,通过使用更优选的nphb底物1,6二羟基萘(1,6dhn)来测试无细胞系统对共底物异戊二烯化的能力。当从2.5mm1,6dhn和500mm葡萄糖开始时,获得约400mg/l(1.3mm)的异戊二烯化的产物。但是,当起始1,6dhn浓度从2.5mm增加到5mm时,最终滴度降低2倍,这表明1,6dhn抑制一种或多种酶。酶测定揭示,大肠杆菌丙酮酸脱氢酶(ecpdh)不仅被1,6dhn抑制,而且还被几种其它芳族聚酮化合物抑制(图2b)。在1mm的1,6dhn、油橄榄醇或白藜芦醇,pdh的活性降低了2倍(图2b)。因此,设计了通过实施pdh旁路来消除pdh的实验(参见图1a和2b)。在pdh旁路中,使用丙酮酸氧化酶(pyox)和乙酰基磷酸转移酶(pta)将丙酮酸转化为乙酰辅酶a,从而消除pdh(图1a)。如在图2a中所示,当从5mm1,6dhn开始时,新系统消除了在较高1,6dhn浓度下所见的抑制,并使5-异戊二烯基-1,6dhn的滴度比pdh系统高4倍(图2b)。图2c显示了利用pdh旁路从5mm1,6dhn开始的5-异戊二烯基-1,6dhn生物合成的时程。在最初的24小时内转化了大约50%的1,6dhn,最终达到705±12mg/l的最终滴度。
nphb对芳族聚酮化合物的异戊二烯化被认为是通过碳阳离子中间体进行,其中第一步是将二磷酸酯与gpp解离,以在gpp的c1碳上生成碳阳离子,其随后攻击附近的亲核体。为了提高异戊二烯基转移的区域特异性,使用与1,6dhn、mg2+和不可水解的gpp类似物(香叶基s-硫羟二磷酸酯)形成复合物的nphb的晶体结构作为起始点(pdbid1zb6;蛋白数据库参照1zb6),将oa模型化进nphb的活性位点。对于设计,使用1,6dhn作为引导物将oa放入结合口袋中,将期望的异戊二烯化位点(oa的c3碳)定位在新生的香叶基c1碳阳离子以上
为了减少要进行实验测试的变体的数目,使用评分系统将可能对oa结合具有最显著影响的变化进行排序。挑选一组代表性的变体(表1),并在其它突变的背景下将每个残基系统化地变回野生型侧链,并在能量评分中评价变化(表2)。y288替代对能量评分的影响最大,因此在每个实验评价的构建体中使用了y288a或y288n突变。突变的频率、多个突变可能如何协同工作、以及用于进一步塑造nphb文库的计算能量评分都被考虑在内。考虑到这些因素,如表1所示,生成了一个文库,该文库包含29种构建体,范围从单点突变体到每个构建体最多6个突变(也参见seqidno:1-29;注意seqidno:1-29包括来自表达构建体的六组氨酸前导序列,即对生物活性不是必需的氨基酸1-20)。
表1:提供了相对于野生型(即,seqidno:30的多肽)的示例性突变和倍数改善。nphb文库构建体和突变(参考seqidno:30的氨基酸位置)。
表2:nphb突变体的动力学参数
bdivarinicacid的动力学参数
本文描述了用于产生和分离本公开内容的经修饰的nphb多肽的重组方法。除了重组生产外,通过使用固相技术的直接肽合成也可以产生多肽(例如,stewart等人(1969)solid-phasepeptidesynthesis(whfreemanco,sanfrancisco);和merrifield(1963)j.am.chem.soc.85:2149-2154;它们中的每一篇通过引用并入)。可以使用手工技术或通过自动化进行肽合成。可以实现自动化的合成,例如,根据制造商提供的说明,使用appliedbiosystems431a肽合成仪(perkinelmer,fostercity,calif.)。
获得了粗纯化的nphb突变体,并使用对于野生型nphb而言饱和的浓度的gpp和oa进行用于cbga生产的初始筛选。鉴定出六种与wtnphb相比具有>10倍的表观活性增加的构建体(m1、m2、m3、m6、m10和m15)和4种与wtnphb相比具有2-10倍表观改善的构建体(m5、m7、m12和m20),而其余的构建体具有与wtnphb相似的活性。将来自初始筛选的顶部命中(m1、m3、m10和m15)纯化并更仔细地表征(图3b)。从初始筛选可以明显看出以下观察结果:(1)y288a(m1)和y288n(m2)本身显著增强了活性,如通过计算所预测的;(2)y288n在任何构建体中的存在降低了纯化产率,表明y288n可能是不稳定的突变,使y288a成为更期望的突变;(3)g286s在y288n(m10)背景中的添加似乎比y288n(m2)进一步提高了活性,从而提示g286s可能是另一种有利的突变;(4)y288a/f213n/a232s(m15)与y288a(m1)相比活性略有提高,即使f213n在y288a/f213n(m5)构建体中具有中性或有害作用,表明a232s也可能是有利的突变。
从这些初步观察结果,设计了一个聚焦文库,其包括各种组合的变体y288a、gs86s和a232s。添加了与y288v的其它组合,其原理是它可能提高稳定性,同时仍然减小y288侧链的尺寸。在一小时的终点测定中,第二个文库中除一个构建体外的所有构建体均表现出比wtnphb高至少100倍的活性。来自第一轮的最佳突变体与来自第二轮的最佳突变体的对比显示在图3b中。显然,来自第一轮的有益突变的组合改善了cbga生产。另外,与y288n相比,y288a和y288v构建体改善了nphb的表达,而没有牺牲活性。
进一步表征了来自初始筛选的最佳两种突变体以及来自聚焦文库的最佳三种构建体。动力学参数总结在表2中。尽管所有突变体具有相对不大的对km的影响,但观察到kcat值的显著改善。m23(seqidno:23的nphb)特别地将kcat提高了750倍,从0.0021±0.00008min-1提高至1.58±0.05min-1。与野生型酶相比,m23和m31的催化效率(kcat/km)提高了1000倍以上。尽管m31具有比m23更高的kcat/km,但使用m23而不是m31,因为m23具有更高的kcat,并且合成生物化学系统通常在饱和oa条件下运行。
设计的突变体m23不仅显示出急剧提高的对oa的异戊二烯化的催化效率,而且还是非常特异性的,仅产生正确的cbga产物。wtnphb产生cbga,但是主要产物是异戊二烯化的异构体(图3c)。相反,设计的突变体m23几乎只能制成cbga。总体而言,设计的酶是比非特异性的异戊二烯化野生型酶远远更有效的cbga合酶。
本公开内容因此提供了突变体nphb变体,其包含:(i)seqidno:30且具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸;(ii)seqidno:30,其具有至少y288x突变,其中x是a、n、s、v或非天然的氨基酸,和至少一个选自v49z1、f213z2、a232s、i234t、v271z3和/或g286s的其它突变,其中z1是s、n、t或g,z2是h、n或g且z3是n或h;(iii)在表1中所示的突变组合中的任一种;(iv)(i)、(ii)或(iii)中的任一个,其包含1-20(例如,2、5、10、15或20;或1-20之间的任何值)个保守氨基酸置换且具有nphb活性;(v)与seqidno:1-29或30具有至少85%、90%、95%、98%或99%同一性且至少具有在(i)、(ii)或(iii)中列举的突变的序列;(vi)从氨基酸21开始包含在seqidno:1-28或29中列举的序列中的任一个的nphb突变;或(vii)与seqidno:1-28或29中的任一个具有至少99%同一性且具有nphb活性的任何序列。“nphb活性”是指酶使底物异戊二烯化、和更具体地从oa产生cbga的能力。
本文中使用的非天然的氨基酸表示在自然界中不存在的氨基酸,诸如n-甲基氨基酸(例如,n-甲基l-丙氨酸、n-甲基l-缬氨酸等)或α-甲基氨基酸、β-同型氨基酸、同型氨基酸和d-氨基酸。在一个特定实施方案中,可用于本公开内容中的非天然氨基酸包括小的疏水的非天然氨基酸(例如,n-甲基l-丙氨酸、n-甲基l-缬氨酸等)。
另外,本公开内容提供了编码前述nphb变体中的任一个的多核苷酸。因为遗传密码的简并性,实际的编码序列可以变化,同时仍然到达为nphb突变体和变体列举的多肽。在seqidno:66、67和68中提供了示例性的多核苷酸序列(分别对应于seqidno:23、29和69的多肽序列)。再次显而易见的是,遗传密码的简并性将允许与seqidno:66、67和68的同一性百分比的广泛变化,同时仍编码seqidno:23、29和69的多肽。
本公开内容还提供了包含本公开内容的任何nphb变体酶的重组宿主细胞和无细胞系统。在一些实施方案中,使用所述重组细胞和无细胞系统进行异戊二烯化过程。
本公开内容的一个目的是,从葡萄糖或戊二烯醇和/或异戊二烯醇生产前体gpp,然后可以将其用于用本公开内容的突变体nphb对添加的oa进行异戊二烯化,从而产生cbga。
本公开内容因此提供了一种无细胞系统,其包括多个将葡萄糖转化为香叶基焦磷酸酯的酶促步骤,其中所述途径包括净化阀和pdh旁路酶促过程。
如图1b中所描绘,本公开内容的一种途径包括使用己糖激酶将葡萄糖转化为葡萄糖-6-磷酸。己糖激酶(ec2.7.1.1)是将己糖(六碳糖)磷酸化从而形成己糖磷酸酯的酶。己糖激酶具有将无机磷酸酯基团从atp转移至底物的能力。已经克隆并表达了来自各种生物的许多己糖激酶蛋白。在一些实施方案中,己糖激酶包含来自酿酒酵母(saccharomycescerevisiae,sc)的在uniprotkb登录号p04806中所示的序列(通过引用并入本文)以及与其具有至少60%、70%、80%、85%、90%、95%、98%、99%同一性且具有己糖激酶活性的序列。
然后葡萄糖-6-磷酸被磷酸葡萄糖异构酶(pgi)(ec5.3.1.9)转化为果糖-6-磷酸。因此,除上述内容外,术语“磷酸葡萄糖异构酶”或“pgi”表示能够催化从葡萄糖-6-磷酸形成果糖-6-磷酸的蛋白,并且它们与seqidno:31具有至少约40%、45%、50%、55%、60%、65%、70%、75%、80%、85%、90%、95%、96%、97%、98%、99%或更大序列同一性,或至少约50%、60%、70%、80%、90%、95%、96%、97%、98%、99%或更大的序列相似性,如通过ncbiblast使用默认参数所计算的,并且其中所述酶具有磷酸葡萄糖异构酶活性。
在另一个或其它实施方案中,本文提供的系统或重组微生物包括磷酸果糖激酶(pfk,多磷酸酯依赖性的pfk或其同系物或变体)的表达。该表达可以与代谢途径中的其它酶组合。pfk可以衍生自嗜热脂肪土芽孢杆菌(g.stearothermophilus)(seqidno:32)。在另一个实施方案中,可以使用pfk的经工程改造的变体,只要它具有磷酸果糖激酶活性且可以将果糖-6-磷酸转化为果糖-1,6-二磷酸。这样的经工程改造的变体可以通过定位诱变、定向进化等获得。因此,在本公开内容中包括与seqidno:32中所示的序列具有至少85-99%同一性并且具有磷酸果糖激酶活性的多肽(参见,例如,seqidno:33-34)。
除前述内容外,术语“果糖1,6二磷酸醛缩酶”或“fba”表示能够催化从果糖1,6-二磷酸形成二羟基丙酮磷酸和甘油醛-3-磷酸的蛋白,并且其与seqidno:35具有至少约40%、45%、50%、55%、60%、65%、70%、75%、80%、85%、90%、95%、96%、97%、98%、99%或更大序列同一性、或至少约50%、60%、70%、80%、90%、95%、96%、97%、98%、99%或更大序列相似性,如通过ncbiblast使用默认参数所计算的。另外的同系物包括:与seqidno:35具有26%同一性的细长聚球蓝细菌(synechococcuselongatus)pcc6301yp_170823.1;与seqidno:35具有80%同一性的黑美人弧菌(vibrionigripulchritudo)atcc27043zp_08732298.1;与seqidno:35具有76%同一性的白色甲基微菌(methylomicrobiumalbum)bg8zp_09865128.1;与seqidno:35具有25%同一性的荧光假单胞菌(pseudomonasfluorescens)pf0-1yp_350990.1;和与seqidno:35具有24%同一性的methylobacteriumnodulansors2060yp_002502325.1。因此,本公开内容包括与seqidno:35具有26%至100%同一性的多肽的用途,其中所述多肽具有二磷酸醛缩酶活性。与前述登录号相关的序列通过引用并入本文。
除前述内容外,术语“磷酸丙糖异构酶”或“tpi”表示能够催化从二羟基丙酮磷酸(dhap)形成甘油醛-3-磷酸的蛋白,并且其与seqidno:36具有至少约40%、45%、50%、55%、60%、65%、70%、75%、80%、85%、90%、95%、96%、97%、98%、99%或更大序列同一性、或至少约50%、60%、70%、80%、90%、95%、96%、97%、98%、99%或更大序列相似性,如通过ncbiblast使用默认参数所计算的。另外的同系物包括:与seqidno:36具有45%同一性的褐家鼠(rattusnorvegicus)aaa42278.1;与seqidno:36具有45%同一性的智人(homosapiens)aah17917.1;与seqidno:36具有40%同一性的枯草芽孢杆菌(bacillussubtilis)best7613np_391272.1;与seqidno:36具有40%同一性的细长聚球蓝细菌(synechococcuselongatus)pcc6301yp_171000.1;和与seqidno:36具有98%同一性的肠道沙门氏菌肠道亚种typhi株血清变型(salmonellaentericasubsp.entericaserovartyphistr.)ag3zp_06540375.1。因此,本公开内容包括与seqidno:36具有40%至100%同一性且具有磷酸丙糖异构酶活性的多肽的用途。与前述登录号相关的序列通过引用并入本文。
在所述途径的另一个步骤中,可以将甘油醛-3-磷酸转化为1,3-二磷酸甘油酸酯。该酶促步骤可以包括“净化阀系统”(如在本文别处所讨论的)。例如,甘油醛-3-磷酸脱氢酶(gap,tdh)将甘油醛-3-磷酸转化为1,3-二磷酸-甘油酸酯。在一个实施方案中,使用用nad+作为辅因子的野生型gap(参见,例如,seqidno:37)或包含p191d突变的突变体gap(相对于seqidno:37的序列,和如在seqidno:38中所示)。在另一个实施方案中,使用突变体gap(mgap;例如,具有d34a/l35r/t35k突变;相对于seqidno:37的序列和如在seqidno:39中所示),其使用nadp+作为辅因子。在另一个实施方案中,使用gap和mgap的组合(gapm6)。当使用优先使用nad+的野生型gap或p118d突变体gap时,包含产生水的nadh氧化酶(noxe)的分子净化阀可用于再循环(“净化”)nadh,所述nadh氧化酶特异性地氧化nadh、但不氧化nadph。
除前述内容外,术语“nadh氧化酶”或“noxe”表示能够将nadh氧化成nad+的蛋白,并且其与seqidno:18具有至少约40%、45%、50%、55%、60%、65%、70%、75%、80%、85%、90%、95%、96%、97%、98%、99%或更大序列同一性、或至少约50%、60%、70%、80%、90%、95%、96%、97%、98%、99%或更大序列相似性,如通过ncbiblast使用默认参数所计算的。
所述途径通过使用磷酸甘油酸激酶(ec2.7.2.3)(pgk;例如,如在seqidno:40,或与其具有至少80%同一性的其同系物或变体中提供的)可以将1,3-二磷酸甘油酸酯进一步转化成3-磷酸甘油酸酯,所述磷酸甘油酸激酶催化磷酸酯基团从1,3-二磷酸甘油酸酯(1,3-bpg)至adp的可逆转移,从而产生3-磷酸甘油酸酯(3-pg)和atp。使用例如gtpase或其它酶或其同系物或变体,用于atp的分子净化阀可以呈现用于再循环adp。
3-磷酸甘油酸酯然后可以被磷酸甘油酸酯变位酶(pgm;例如,如在seqidno:41,或与其具有至少80%同一性的其同系物或变体中提供的)转化成2-磷酸甘油酸酯。
烯醇化酶(eno;例如,如在seqidno:42,或与其具有至少80%同一性的其同系物或变体中提供的)然后可以将2-磷酸甘油酸酯转化成磷酸烯醇丙酮酸(pep)。
丙酮酸激酶(pyk;例如,如在seqidno:43、44和45,或与seqidno:43、44或45中的任一个具有至少80%同一性的其同系物或变体中提供的)将pep转化成丙酮酸。
如上所提及,丙酮酸脱氢酶(pdh)被所述途径的产物抑制。因此,可以使用pdh旁路将丙酮酸转化为乙酰辅酶a。pdh旁路包括两个酶促步骤:(i)由丙酮酸氧化酶(例如,来自绿色气球菌(aerococcusviridans)的pyox;ec1.2.3.3;参见seqidno:46)催化的丙酮酸→乙酰基磷酸酯;和(ii)由乙酰基磷酸转移酶(又名磷酸乙酰基转移酶)(例如,来自嗜热脂肪土芽孢杆菌的pta)催化的乙酰基磷酸酯→乙酰辅酶a。
如本文中使用的,在本公开内容的组合物和方法中使用的pyox包括与seqidno:46具有至少85%、90%、95%、98%、99%同一性并且具有丙酮酸氧化酶活性的序列。
磷酸乙酰基转移酶(ec2.3.1.8)是一种催化乙酰辅酶a+磷酸酯至辅酶a+乙酰基磷酸酯的化学反应的酶,且反之亦然。磷酸乙酰基转移酶由pta在大肠杆菌中编码。pta参与乙酸向乙酰辅酶a的转化。具体而言,pta催化乙酰辅酶a向乙酰基磷酸酯的转化。pta同系物和变体是已知的。在ncbi上可得到大约1075种细菌磷酸乙酰基转移酶。例如,这样的同系物和变体包括:磷酸乙酰基转移酶pta(猫立克次氏体(rickettsiafelis)urrwxcal2)gi|67004021|gb|aay60947.1|(67004021);磷酸乙酰基转移酶(蚜虫巴克纳氏菌(buchneraaphidicola)cc(cinaracedri)株)gi|116256910|gb|abj90592.1|(116256910);pta(蚜虫巴克纳氏菌cc(cinaracedri)株)gi|116515056|ref|yp_802685.1|(116515056);pta(glossinabrevipalpis的wigglesworthiaglossinidia内共生体)gi|25166135|dbj|bac24326.1|(25166135);pta(多杀巴斯德氏菌多杀亚种pm70株(pasteurellamultocidasubsp.multocidastr.pm70))gi|12720993|gb|aak02789.1|(12720993);pta(深红红螺菌(rhodospirillumrubrum))gi|25989720|gb|aan75024.1|(25989720);pta(威氏李斯特菌6b血清变型slcc5334株(listeriawelshimeriserovar6bstr.slcc5334))gi|116742418|emb|cak21542.1|(116742418);pta(鸟分枝杆菌副结核亚种k-10(mycobacteriumaviumsubsp.paratuberculosisk-10))gi|41398816|gb|aas06435.1|(41398816);磷酸乙酰基转移酶(pta)(布氏疏螺旋体(borreliaburgdorferi)b31)gi|15594934|ref|np_212723.1|(15594934);磷酸乙酰基转移酶(pta)(布氏疏螺旋体b31)gi|2688508|gb|aab91518.1|(2688508);磷酸乙酰基转移酶(pta)(流感嗜血菌(haemophilusinfluenzae)rdkw20)gi|1574131|gb|aac22857.1|(1574131);磷酸乙酰基转移酶pta(rickettsiabelliirml369-c)gi|91206026|ref|yp_538381.1|(91206026);磷酸乙酰基转移酶pta(rickettsiabelliirml369-c)gi|91206025|ref|yp_538380.1|(91206025);磷酸乙酰基转移酶pta(结核分枝杆菌(mycobacteriumtuberculosis)f11)gi|148720131|gb|abr04756.1|(148720131);磷酸乙酰基转移酶pta(结核分枝杆菌haarlem株)gi|134148886|gb|eba40931.1|(134148886);磷酸乙酰基转移酶pta(结核分枝杆菌c)gi|124599819|gb|eay58829.1|(124599819);磷酸乙酰基转移酶pta(rickettsiabelliirml369-c)gi|91069570|gb|abe05292.1|(91069570);磷酸乙酰基转移酶pta(rickettsiabelliirml369-c)gi|91069569|gb|abe05291.1|(91069569);磷酸乙酰基转移酶(pta)(苍白密螺旋体苍白亚种nichols株(treponemapallidumsubsp.pallidumstr.nichols))gi|15639088|ref|np_218534.1|(15639088);和磷酸乙酰基转移酶(pta)(苍白密螺旋体苍白亚种nichols株)gi|3322356|gb|aac65090.1|(3322356),与登录号相关的每个序列通过引用整体并入本文。
再次转向图1b,所述途径包括乙酰辅酶a向乙酰乙酰辅酶a的转化。乙酰辅酶a向乙酰乙酰辅酶a的转化由乙酰辅酶a乙酰基转移酶(例如,phaa)执行。许多乙酰辅酶a乙酰基转移酶是本领域已知的。例如,来自富养产碱菌(r.eutropha)的乙酰辅酶a乙酰基转移酶。在另一个实施方案中,所述乙酰辅酶a乙酰基转移酶具有与seqidno:47具有至少85%、90%、95%、98%、99%或100%同一性的氨基酸序列。
乙酰乙酰辅酶a和乙酰辅酶a可以被具有a110g突变的酶hmg-coa合酶(参见,例如,seqidno:48)或与其具有85%-99%序列同一性的其同系物或变体转化为hmg-coa。
然后通过nadph和hmg-coa还原酶(参见,例如,seqidno:49)或与其具有85%-99%序列同一性的其同系物或变体的作用,将hmg-coa还原成甲羟戊酸。
甲羟戊酸然后通过atp和甲羟戊酸激酶(mvk)的作用而磷酸化以产生甲羟戊酸-5-磷酸和adp。甲羟戊酸激酶是本领域已知的且包括与seqidno:50的序列具有至少85-100%(例如,85%、90%、95%、98%、99%)同一性且具有甲羟戊酸激酶活性的序列。
甲羟戊酸-5-磷酸通过atp和磷酸甲羟戊酸激酶(pmvk)的作用而进一步磷酸化以产生甲羟戊酸-5-二磷酸和adp。磷酸甲羟戊酸激酶是本领域已知的且包括与seqidno:51的序列具有至少85-100%(例如,85%、90%、95%、98%、99%)同一性且具有磷酸甲羟戊酸激酶活性的序列。
甲羟戊酸-5-二磷酸通过atp和二磷酸甲羟戊酸脱羧酶(mdc)的作用而脱羧以产生adp、co2和异戊基焦磷酸酯。二磷酸甲羟戊酸脱羧酶是本领域已知的且包括与seqidno:52的序列具有至少85-100%(例如,85%、90%、95%、98%、99%)同一性且具有二磷酸甲羟戊酸激酶活性的序列。
可以使用各种其它甲羟戊酸途径(参见,例如,图7)。
然后,在相对于seqidno:53具有s82f突变的法呢基-pp合酶存在下,从dmapp和异戊基焦磷酸酯的组合形成香叶基焦磷酸酯(gpp)。在一个实施方案中,法呢基-二磷酸合酶具有与具有s82f突变的seqidno:53具有至少95%、98%、99%或100%同一性的序列,且其能够从dmapp和异戊基焦磷酸酯形成香叶基焦磷酸酯。
gpp然后可以用作许多途径的底物,所述途径导致产生异戊二烯基-黄酮类化合物、香叶基-flavonoics、异戊二烯基-芪类化合物、香叶基-芪类化合物、cbga、cbgva、cbda、cbdva、cbgva、cbcva、thca和thcva(参见,例如,fig.1a)。
例如,如上所述,使用nphb突变体(例如,m23突变体),使用包括pdh旁路的完全合成生物化学系统测试了从葡萄糖和oa直接产生cbga的能力(参见,图1a和图1b)。在系统中使用m23的初始生产力为67mgl-1hr-1,其中最终滴度为744±34mgl-1的cbga。这比使用wtnphb的cbga生产快100倍,并达到高21倍的滴度。应当指出,使用突变体nphb酶,在24小时内达到最大滴度,并且生产停止,但是使用野生型酶,系统连续运行长达4天,这表明所述酶和辅因子在更长的时间段内保持活性和活力。注意到一旦产生了约500mgl-1cbga,反应就变得浑浊。收集沉淀物,并通过sds-page分析来鉴定沉淀物中的酶混合物,表明溶液中高水平的cbga造成酶沉淀。开发了一种更有效的系统以在反应过程中移取产物。
尽管在反应中使用壬烷覆盖物来提取cbga,但是cbga比壬烷更易溶于水,这限制了可以用简单覆盖物提取的cbga的量。因此,设计了一种流动系统,该系统将从壬烷层捕获cbga并将其捕集在单独的水蓄池中(图4b)。通过实施该流动系统,将较低浓度的cbga维持在反应容器中以减轻酶沉淀。该流动系统确实将最终滴度提高到1.2g/l。
然后进行实验以通过用divirinicacid(da)代替系统中的oa来产生许多稀有大麻素的前体cbgva(参见,例如,图1b)。首先测试设计的酶以确定它们是否对da底物有活性。测试了两种最佳突变体m23和m31以及wtnphb的产生cbgva的能力。表2中显示的动力学数据表明,m31远远更优,其催化效率比m23高15倍,并且比wtnphb高650倍。因此,进一步的努力利用m31从葡萄糖和divarinicacid生产cbgva。如在图4a中所示,cbgva以约107mgl-1hr-1的最大生产力生产,并达到1.74±0.09gl-1的最终滴度,将92%的添加的divarinicacid转化成cbgva。cbgva的生产不需要壬烷流动系统,因为cbgva在沉淀酶中的功效较小。
为了证明该方法最终可以用于制备其它大麻素,使用cbda合酶将cbga转化为cbda,并将cbgva转化为cbdva。对于cbda,壬烷覆盖物含有大量的cbga,因此通过简单地将壬烷覆盖物转移至包含cbda合酶的溶液,cbga就以14.4±0.8mgl-1小时-1mg总蛋白-1的恒定速率转化为cbda保持4天。
由于cbgva在壬烷中的有限溶解度,因此将cbgva提取并添加到含有cbda合酶的反应中。使用gc-ms,cbda合酶的产物实际上是cbdva。
本公开内容因此提供了一种用于生产gpp的无细胞系统。进一步,本公开内容提供了一种无细胞方法,其用于如下生产一系列纯的大麻素和其它异戊二烯化的天然产物:使用与突变体nphb组合的gpp途径,或使用本公开内容的突变体nphb的底物。该方法的成功使用了本公开内容的经工程改造的异戊二烯基转移酶(例如,如上所述的nphb突变体),该酶是有活性的,高特异性的,且消除了对天然跨膜异戊二烯基转移酶的需要。本文提供的生物化学合成平台的模块性和灵活性具有基于生物的方法的益处,但消除了令人满意的生命系统的复杂性。例如,gpp毒性不影响设计过程。此外,oa不被酵母吸收,因此外源添加oa的方法在细胞中不一定是可能的。实际上,无细胞系统的灵活性可以极大地促进进一步优化、另外途径酶以及试剂和辅因子修饰所需的设计-构建-测试循环。
转向图1的总途径,本公开内容提供了由酶催化的许多步骤以将“底物”转化成产物。在一些情况下,一个步骤可以利用辅因子,但是一些步骤不使用辅因子(例如,nad(p)h,atp/adp等)。表3提供了所使用的酶、生物和反应量以及登录号的列表(与此类登录号相关的序列通过引用并入本文)。
表3:在酶促平台中使用的酶
如上所述,通过本文和上面描述的突变体nphb多肽的活性,进行gpp对油橄榄醇酯的异戊二烯化。
本公开内容提供了生产异戊二烯化的化合物的体外方法,且此外,提供了用于生产大麻素和大麻素前体(例如,cbga、cbgva或cbgxa,其中‘x’表示任何化学基团)的体外方法。在本公开内容的一个实施方案中,无细胞制剂可以通过例如三种方法制备。在一个实施方案中,如本文所述,购买所述途径的酶并在合适的缓冲液中混合,并添加合适的底物,并在适合生产异戊二烯化的化合物或大麻素或大麻素前体(视情况而定)的条件下温育。在一些实施方案中,所述酶可以结合至支持物或在噬菌体展示或其它表面表达系统中表达,并且例如,固定在与代谢途径的循环中的点相对应的流体途径中。
图5a-b将途径描绘为各种“模块”(例如,糖酵解模块、甲羟戊酸/类异戊二烯模块、大麻素模块、聚酮化合物模块)。例如,类异戊二烯模块通过甲羟戊酸途径从乙酰辅酶a产生类异戊二烯香叶基焦磷酸酯(gpp)。芳族聚酮化合物模块利用iii型聚酮化合物合酶(pks)将己酰基辅酶a和丙二酰基辅酶a(源自乙酰辅酶a)转化成油橄榄醇酸(oa)。大麻素模块使用来自类异戊二烯模块和聚酮化合物模块的产物以得到大麻萜酚酸,其然后通过大麻素合酶转化为最终的大麻素。
在另一个实施方案中,在表达所述酶的条件下,将编码所述途径的一种或多种酶的一种或多种多核苷酸克隆到一种或多种微生物中。随后将细胞裂解,并将含有一种或多种衍生自细胞的酶的裂解制剂与合适的缓冲液和底物(如果必要的话,以及所述途径的一种或多种其它酶)组合,以生成异戊二烯化的化合物或大麻素或大麻素前体。可替换地,可以从裂解制剂中分离酶,且然后在适当的缓冲液中重组。在又一个实施方案中,使用购买的酶和表达的酶的组合在适当的缓冲液中提供途径。在一个实施方案中,克隆并表达所述途径的热稳定的多肽/酶。在一个实施方案中,所述途径的酶衍生自嗜热微生物。然后将微生物裂解,将制剂加热至一定温度,在该温度,所述途径的热稳定多肽是有活性的,且其它多肽(不感兴趣的多肽)被变性并变为无活性的。因此,该制剂包括微生物中所有酶的子集,且包括有活性的热稳定酶。然后该制剂可用于实现所述途径以生产异戊二烯化的化合物或大麻素或大麻素前体。
例如,为了构建一个体外系统,所有的酶可从市场上获得或通过亲和色谱法纯化,测试活性,并且在适当地选择的反应缓冲液中混合在一起。
还设想了体内系统,其在被工程改造进微生物中的生物合成途径中使用前述酶的全部或部分来获得重组微生物。
本公开内容还提供了包含代谢工程改造的生物合成途径的重组生物,所述途径包含用于生产异戊二烯化的化合物的突变体nphb,并且本公开内容可以进一步包括一种或多种表达用于生产大麻素的酶的其它生物(例如,一组表达部分途径的微生物和第二组表达所述途径的另一部分或最终部分等的微生物等的共培养物)。
在一个实施方案中,本公开内容提供了一种重组微生物,其包含与亲本微生物相比升高的至少一种靶酶的表达,或编码在亲本生物中未发现的酶。在另一个或其它实施方案中,所述微生物包含至少一种编码酶的基因的减少、破坏或敲除,所述酶与产生期望的代谢物所必需的代谢物竞争或其产生不希望的产物。重组微生物表达一种酶,该酶产生至少一种参与生物合成途径的代谢物,所述生物合成途径用于生产例如异戊二烯化的化合物或大麻素或大麻素前体。一般而言,重组微生物包含至少一种重组代谢途径,其包含靶酶,并且可以进一步包括在竞争性生物合成途径中的酶的活性或表达的降低。所述途径起作用以在例如异戊二烯化的化合物或大麻素或大麻素前体的生产中修饰底物或代谢中间体。所述靶酶由衍生自合适的生物学来源的多核苷酸编码并由其表达。在一些实施方案中,所述多核苷酸包含衍生自细菌或酵母来源并重组工程改造进本公开内容的微生物中的基因。在另一个实施方案中,编码期望的靶酶的多核苷酸天然存在于生物体中,但是被重组工程改造以与天然表达水平相比过表达。
术语“微生物”包括来自古细菌域、细菌域和真核生物域的原核和真核微生物物种,所述真核生物域包括酵母和丝状真菌、原生动物、藻类或高级原生生物。术语“微生物细胞”和“微生物”与术语微生物互换使用。
术语“原核生物”是本领域公知的,并且表示不包含细胞核或其它细胞器的细胞。通常将原核生物分类为细菌和古细菌两个域之一。古细菌域和细菌域的生物之间的决定性差异是基于16s核糖体rna中的核苷酸碱基序列的根本差异。
“细菌”或“真细菌界”表示原核生物域。细菌包括如下至少11个不同的组:(1)革兰氏阳性(gram+)细菌,其中存在两个主要小类:(1)高g+c组(放线菌属(actinomycetes)、分枝杆菌属(mycobacteria)、微球菌属(micrococcus)等);(2)低g+c组(芽孢杆菌属(bacillus)、梭状芽胞杆菌属(clostridia)、乳杆菌属(lactobacillus)、葡萄球菌属(staphylococci)、链球菌属(streptococci)、支原体属(mycoplasmas));(2)变形菌(proteobacteria),例如,紫色光合的+非光合的革兰氏阴性细菌(包括大多数“常见的”革兰氏阴性细菌);(3)蓝细菌(cyanobacteria),例如氧化性光能利用菌;(4)螺旋体属(spirochetes)和有关的物种;(5)浮霉状菌属(planctomyces);(6)拟杆菌属(bacteroides),黄杆菌属(flavobacteria);(7)衣原体属(chlamydia);(8)绿硫细菌;(9)绿色非硫细菌(也称作厌氧性光能利用菌);(10)耐辐射微球菌(radioresistantmicrococci)和有关的物种;和(11)栖热袍菌属(thermotoga)和嗜热栖热腔菌(thermosiphothermophiles)。
“革兰氏阴性细菌”包括球菌、非肠道杆菌和肠道杆菌。革兰氏阴性细菌的属包括例如奈瑟球菌属(neisseria)、螺菌属(spirillum)、巴斯德氏菌属(pasteurella)、布鲁杆菌属(brucella)、耶尔森氏菌属(yersinia)、弗朗西丝氏菌属(francisella)、嗜血菌属(haemophilus)、博德特氏菌属(bordetella)、埃希氏菌属(escherichia)、沙门氏菌属(salmonella)、志贺氏菌属(shigella)、克雷伯氏菌属(klebsiella)、变形菌属(proteus)、弧菌属(vibrio)、假单胞菌属(pseudomonas)、拟杆菌属(bacteroides)、醋杆菌属(acetobacter)、气杆菌属(aerobacter)、土壤杆菌属(agrobacterium)、固氮菌属(azotobacter)、螺旋状菌属(spirilla)、沙雷氏菌属(serratia)、弧菌属(vibrio)、根瘤菌属(rhizobium)、衣原体属(chlamydia)、立克次氏体属(rickettsia)、密螺旋体属(treponema)和梭杆菌属(fusobacterium)。
“革兰氏阳性细菌”包括球菌、不形成孢子的杆菌和形成孢子的杆菌。革兰氏阳性细菌的属包括例如放线菌属(actinomyces)、芽孢杆菌属(bacillus)、梭菌属(clostridium)、棒杆菌属(corynebacterium)、丹毒丝菌属(erysipelothrix)、乳杆菌属(lactobacillus)、李斯特菌属(listeria)、分枝杆菌属(mycobacterium)、粘球菌属(myxococcus)、诺卡氏菌属(nocardia)、葡萄球菌属(staphylococcus)、链球菌属(streptococcus)和链霉菌属(streptomyces)。
如本文中使用的,酶的“活性”是其催化产生代谢物的反应(即,“发挥功能”)的能力的量度,并且可以表示为产生反应的代谢物的速率。例如,酶活性可以表示为每单位时间或每单位酶产生的代谢物的量(例如,浓度或重量),或以亲和力或解离常数表示。
术语“生物合成途径”也被称作“代谢途径”,表示一组用于将一种化学物质转化(转变)成另一种的合成代谢或分解代谢生物化学反应(参见,例如,图1a-b)。如果基因产物平行地或串联地作用于相同的底物、产生相同的产物、或作用于或产生相同的底物和代谢物终产物之间的代谢中间体(即,代谢物),则所述基因产物属于相同的“代谢途径”。本公开内容提供了具有用于生产期望的产物或中间体的代谢工程改造的途径的重组微生物。
因此,如下生产代谢“工程改造的”或“修饰的”微生物:将遗传物质引入选择的宿主或亲本微生物中,从而修饰或改变该微生物的细胞生理学和生物化学。通过遗传物质的引入,亲本微生物获得新的特性,例如产生新的或更大量的细胞内代谢物或表达通常不表达的多肽的能力。在一个示例性实施方案中,遗传物质向亲本微生物中的引入导致新的或经修饰的能力以使用丙酮酸氧化酶和乙酰基磷酸转移酶通过pdh旁路产生乙酰基磷酸酯和/或乙酰辅酶a。引入亲本微生物中的遗传物质含有编码一种或多种酶的基因或部分基因,所述酶参与用于生产异戊二烯化的化合物或大麻素或大麻素前体的生物合成途径,且所述遗传物质也可以包括用于表达这些基因和/或调节这些基因的表达的其它元件,例如启动子序列。
除了将遗传物质引入宿主或亲本微生物中以外或作为替代方案,经工程改造的或修饰的微生物还可以包括基因或多核苷酸的破坏、缺失或敲除,以改变微生物的细胞生理学和生物化学。通过基因或多核苷酸的减少、破坏或敲除,微生物获得新的或改良的特性(例如,产生新的或更大量的细胞内代谢物,改善代谢物沿期望的途径的通量,和/或减少不希望的副产物的产生的能力),或从无细胞制剂消除酶,所述酶可能与从裂解制剂产生的生物合成途径竞争。
“酶”是指通常全部或大部分由构成蛋白或多肽的氨基酸组成的任何物质,其或多或少地特异性地催化或促进一种或多种化学或生物化学反应。
在本文中可互换地使用的术语“蛋白”或“多肽”包含一条或多条称为氨基酸的化学结构单元的链,所述氨基酸通过称为肽键的化学键连接在一起。蛋白或多肽可以作为酶发挥功能。
本文中使用的术语“代谢工程改造的”或“代谢工程改造”涉及在微生物中的合理途径设计,以及生物合成基因、与操纵子相关的基因和这样的多核苷酸的控制元件的组装,以生产期望的代谢物,诸如乙酰基磷酸酯和/或乙酰辅酶a、高级醇或其它化学物质。“代谢工程改造的”可以进一步包括通过使用基因工程改造和适当的培养条件(包括减少、破坏或敲除与通向期望途径的中间体竞争的竞争性代谢途径)调节和优化转录、翻译、蛋白稳定性和蛋白功能来优化代谢通量。生物合成基因可以对于宿主微生物而言是异源的,这是由于对于宿主而言是外来的,或者由于诱变、重组和/或与内源宿主细胞中的异源表达控制序列结合被修饰。在一个实施方案中,在多核苷酸对宿主生物而言是异源的情况下,可以对多核苷酸进行密码子优化。
“代谢物”表示由代谢产生的任何物质,或对于特定代谢过程而言必需的或参与特定代谢过程的物质,所述特定代谢过程产生期望的代谢物、化学物质、醇或酮。代谢物可以是作为代谢的起始材料(例如,葡萄糖等)、中间体(例如,乙酰辅酶a)或终产物(例如,cbda)的有机化合物。代谢物可以用于构建更复杂的分子,或者它们可以分解成更简单的分子。中间代谢物可以从其它代谢物合成,可能用于制备更复杂的物质,或分解成更简单的化合物,这经常伴随化学能的释放。
“突变”是指产生突变蛋白、酶、多核苷酸、基因或细胞的任何过程或机制。这包括其中蛋白、酶、多核苷酸或基因序列被改变的任何突变,以及由这样的突变引起的细胞中的任何可检测的变化。通常,通过点突变、单个或多个核苷酸残基的缺失或插入,在多核苷酸或基因序列中发生突变。突变包括在基因的蛋白编码区内产生的多核苷酸改变,以及在蛋白编码序列之外的区域(例如,但不限于,调节序列或启动子序列)中的改变。基因中的突变可以是“沉默的”,即,不反映在表达后的氨基酸改变中,从而导致基因的“序列保守”变体。当一种氨基酸对应于超过一种密码子时,通常出现这种情况。产生蛋白的不同一级序列的突变可以被称作突变蛋白或蛋白变体。
“天然的”或“野生型”蛋白、酶、多核苷酸、基因或细胞是指在自然界中存在的蛋白、酶、多核苷酸、基因或细胞。
“亲本微生物”表示用于产生重组微生物的细胞。在一个实施方案中,术语“亲本微生物”描述了在自然界中存在的细胞,即未经遗传修饰的“野生型”细胞。术语“亲本微生物”进一步描述用作用于进一步工程改造的“亲本”的细胞。在该后一个实施方案中,细胞可以已经被遗传工程改造,但是用作进一步遗传工程改造的来源。
例如,可以对野生型微生物进行遗传修饰以表达或过表达第一靶酶诸如己糖激酶。该微生物可以在被修饰以表达或过表达第二靶酶(例如,果糖-1,6-二磷酸醛缩酶)的微生物的产生中充当亲本微生物。该微生物又可以被修饰以表达或过表达例如nadh氧化酶和gald-3-磷酸脱氢酶(及其突变体),其可以进一步被修饰以表达或过表达第三靶酶,例如,磷酸甘油酸激酶等。本文中使用的“表达”或“过表达”表示期望的基因产物的表型表达。在一个实施方案中,可以工程改造生物体中天然存在的基因,使得其与异源启动子或调节结构域连接,其中调节结构域引起该基因的表达,从而相对于野生型生物体修饰其正常表达。可替换地,可以工程改造生物体以除去或减少对该基因的阻抑功能,从而修饰其表达。在又一个实施方案中,将包含与期望的表达控制/调节元件可操作地连接的基因序列的盒工程改造到微生物中。
因此,亲本微生物作为连续遗传修饰事件的参考细胞发挥功能。每个修饰事件可以通过将一种或多种核酸分子引入参考细胞来完成。所述引入促进一种或多种靶酶的表达或过表达或一种或多种靶酶的减少或消除。应当理解,术语“促进”涵盖通过遗传修饰(例如亲本微生物中的启动子序列的遗传修饰)来激活编码靶酶的内源多核苷酸。还应当理解,术语“促进”涵盖将编码靶酶的外源多核苷酸引入亲本微生物中。
将编码可用于产生代谢物的酶(包括其同系物、变体、片段、相关融合蛋白或功能等同物)的多核苷酸用在重组核酸分子中,其指导这样的多肽在适当的宿主细胞(诸如细菌或酵母细胞)中表达。本文提供的序列和登录号为本领域技术人员提供了使用容易得到的软件和基础生物学知识来获得和得到本公开内容的各种酶的编码序列的能力。
本文所附的序列表提供了可用于本文所述方法中的示例性多肽。应当理解,不改变多肽分子活性的序列的添加,诸如非功能性或非编码序列(例如,多his标签)的添加,是基本分子的保守变异。
应当理解,本文描述的多核苷酸包括“基因”,并且上述的核酸分子包括“载体”或“质粒”。
术语“多核苷酸”、“核酸”或“重组核酸”表示多核苷酸诸如脱氧核糖核酸(dna),且在适当的情况下,表示核糖核酸(rna)。
关于基因或多核苷酸的术语“表达”表示基因或多核苷酸的转录,和适当的话,得到的mrna转录物向蛋白或多肽的翻译。因此,如从上下文将显而易见,蛋白或多肽的表达源自开放读码框的转录和翻译。
本领域技术人员会认识到,由于遗传密码的简并性质,可以使用其核苷酸序列不同的多种密码子来编码给定的氨基酸。本文提及编码上述生物合成酶或多肽的特定多核苷酸或基因序列仅用于举例说明本公开内容的一个实施方案,并且本公开内容包括任何序列的多核苷酸,所述序列编码包含在本公开内容的方法中使用的酶的多肽和蛋白的相同氨基酸序列的多肽。以类似的方式,多肽通常可以在其氨基酸序列中耐受一个或多个氨基酸置换、缺失和插入,而不损失或显著损失期望的活性。本公开内容包括具有替代氨基酸序列的此类多肽,并且由本文所示的dna序列编码的氨基酸序列仅举例说明本公开内容的示例性实施方案。
如本文其它地方更详细描述的,本公开内容提供了重组dna表达载体或质粒形式的多核苷酸,其编码一种或多种靶酶。通常,此类载体可以在宿主微生物的细胞质中复制,或整合到宿主微生物的染色体dna中。在任一种情况下,载体可以是稳定载体(即,即使仅采用选择压力,载体经多次细胞分裂后仍存在)或瞬时载体(即,随着细胞分裂次数的增加,载体逐渐被宿主微生物遗失)。本公开内容提供了分离形式(即,非纯的,但在制备物中以自然界中未发现的丰度和/或浓度存在)以及纯化形式(即,基本上不含有污染物质,或基本上不含有与相应dna一起存在于自然界中的物质)的dna分子。
使用cdna、mrna或可替换地基因组dna作为模板和适当的寡核苷酸引物,根据标准pcr扩增技术和下面实施例部分中描述的那些程序,可以扩增本公开内容的多核苷酸。可以将如此扩增的核酸克隆到适当的载体中并通过dna序列分析进行表征。此外,通过标准合成技术,例如使用自动化的dna合成仪,可以制备对应于核苷酸序列的寡核苷酸。
本公开内容提供了本申请所附序列表中的许多多肽序列,其可以用于使用遗传密码的简并性或使用公众可得到的数据库搜索编码序列来设计、合成和/或分离多核苷酸序列。
还理解,可以如下产生分离的编码与本文所述酶同源的多肽的多核苷酸分子:向编码特定多肽的核苷酸序列中引入一个或多个核苷酸置换、添加或缺失,使得将一个或多个氨基酸置换、添加或缺失引入编码的蛋白中。通过标准技术,诸如定位诱变和pcr介导的诱变,可以将突变引入多核苷酸中。与那些可能需要进行非保守氨基酸置换的位置相反,在一些位置,优选进行保守氨基酸置换。
如本领域技术人员会理解的,修饰编码序列以增强其在特定宿主中的表达可以是有利的。遗传密码是冗余的,具有64种可能密码子,但大多数生物体通常使用这些密码子的一部分。在物种中最常利用的密码子被称为最佳密码子,而那些不被经常利用的密码子被分类为稀有或利用率低的密码子。密码子可被置换以反映宿主的优选密码子选择,该过程有时被称为“密码子优化”或“控制物种密码子偏爱”。
可以制备含有被特定原核或真核宿主偏爱的密码子的优化编码序列(也参见,murray等人(1989)nucl.acidsres.17:477-508),例如,与由非优化序列产生的转录物相比,提高翻译速率或产生具有期望特性(例如更长的半衰期)的重组rna转录物。翻译终止密码子也可以被修饰以反映宿主偏好。例如,酿酒酵母和哺乳动物的典型终止密码子分别是uaa和uga。单子叶植物的典型终止密码子是uga,而昆虫和大肠杆菌通常使用uaa作为终止密码子(dalphin等人(1996)nucl.acidsres.24:216-218)。用于优化用于在植物中表达的核苷酸序列的方法提供在例如美国专利号6,015,891以及其中引用的参考文献中。
术语“底物”或“合适的底物”表示通过酶的作用转化成或意图转化成另一种化合物的任何物质或化合物。该术语不仅包括单一化合物,而且包括化合物的组合,诸如溶液、混合物和含有至少一种底物的其它物质或其衍生物。此外,术语“底物”不仅包括提供起始材料的化合物,而且包括用在如本文所述的与代谢工程改造的微生物有关的途径中的中间体和终产物代谢物。
“转化”表示将载体引入宿主细胞中的过程。转化(或转导或转染)可以通过许多方式中的任何一种来实现,所述方式包括电穿孔、显微注射、生物弹道技术(或颗粒轰击介导的递送)或土壤杆菌介导的转化。
“载体”通常表示可以在生物体、细胞或细胞组分之间传播和/或转移的多核苷酸。载体包括病毒、细菌噬菌体、原病毒(pro-viruses)、质粒、噬菌粒、转座子和人工染色体诸如yac(酵母人工染色体)、bac(细菌人工染色体)以及plac(植物人工染色体)等,它们是“附加体”,即自主复制或可以整合到宿主细胞的染色体中。载体也可以是裸rna多核苷酸、裸dna多核苷酸、在同一链内由dna和rna组成的多核苷酸、聚赖氨酸缀合的dna或rna、肽缀合的dna或rna、脂质体缀合的dna等,它们在自然界中不是附加型的(episomal),或者其可以是包含一种或多种上述多核苷酸构建体的生物体,诸如土壤杆菌或细菌。
表达载体的各种组分可以广泛变化,取决于载体的预期用途和意图使载体在其中复制或驱动表达的宿主细胞。适于在大肠杆菌、酵母、链霉菌和其它常用细胞中表达基因和维持载体的表达载体组分是广泛已知的和商购可得的。例如,用于包含在本公开内容的表达载体中的合适启动子包括在真核或原核宿主微生物中发挥功能的那些启动子。启动子可以包含调节序列,其允许调节与宿主微生物的生长相关的表达或者响应于化学或物理刺激而使基因的表达开启或关闭。对于大肠杆菌和某些其它细菌宿主细胞,可以使用来源于生物合成酶、赋予抗生素抗性的酶和噬菌体蛋白的基因的启动子,且包括例如半乳糖启动子、乳糖(lac)启动子、麦芽糖启动子、色氨酸(trp)启动子、β-内酰胺酶(bla)启动子、细菌噬菌体λpl启动子和t5启动子。此外,还可以使用合成启动子,诸如tac启动子(美国专利号4,551,433,其通过引用整体并入本文)。对于大肠杆菌表达载体,包括大肠杆菌复制起点(诸如来自puc、p1p、p1和pbr)是有用的。
因此,重组表达载体含有至少一种表达系统,该表达系统又由与启动子可操作地连接的基因编码序列的至少一部分和任选的终止序列组成,所述终止序列起作用以实现编码序列在相容的宿主细胞中的表达。通过用本公开内容的重组dna表达载体转化来修饰宿主细胞,以包含表达系统序列作为染色体外元件或整合到染色体中。
另外,且如上所述,本文提供的微生物和方法包括可用于产生代谢物的酶的同系物。关于第一家族或物种的原始酶或基因使用的术语“同系物”表示第二家族或物种的不同酶或基因,其通过功能、结构或基因组分析被确定为对应于第一家族或物种的原始酶或基因的第二家族或物种的酶或基因。最经常地,同系物将具有功能、结构或基因组相似性。使用遗传探针和pcr可以容易地克隆酶或基因的同系物的技术是已知的。使用功能测定和/或通过基因的基因组作图,可以确认克隆的序列作为同系物的身份。
如果编码蛋白的核酸序列具有与编码第二蛋白的核酸序列相似的序列,则蛋白与第二蛋白具有“同源性”或是“同源的”。可替换地,如果两种蛋白具有“相似的”氨基酸序列,则蛋白与第二蛋白具有同源性。(因此,术语“同源蛋白”定义为表示两种蛋白具有相似的氨基酸序列)。
如本文中使用的,当氨基酸序列具有至少约30%、40%、50%60%、65%、70%、75%、80%、85%、90%、91%、92%、93%、94%、95%、96%、97%、98%或99%同一性时,两种蛋白(或蛋白的区域)是基本上同源的。为了确定两个氨基酸序列或两个核酸序列的同一性百分比,将所述序列比对以达到最佳对比目的(例如,可以在第一和第二氨基酸或核酸序列中的一个或两个中引入缺口用以最佳比对,并且为了对比目的可以忽略不同源的序列)。在一个实施方案中,出于对比目的而比对的参考序列的长度为所述参考序列的长度的至少30%,通常至少40%,更通常至少50%,且甚至更通常至少60%,甚至更通常至少70%、80%、90%、100%。然后对比相应氨基酸位置或核苷酸位置处的氨基酸残基或核苷酸。当第一序列中的位置被与第二序列中相应位置相同的氨基酸残基或核苷酸占据时,则所述分子在该位置是相同的(本文中使用的氨基酸或核酸“同一性”等同于氨基酸或核酸“同源性”)。两个序列之间的同一性百分比是所述序列共有的相同位置的数目的函数,考虑缺口的数目和每个缺口的长度,所述缺口为了两个序列的最佳比对而需要引入。
当“同源的”用于指蛋白或肽时,应当认识到,不相同的残基位置经常由于保守氨基酸置换而不同。“保守氨基酸置换”是这样的置换:其中一个氨基酸残基被置换为另一个含有具有类似化学特性(例如,电荷或疏水性)的侧链(r基团)的氨基酸残基。一般而言,保守氨基酸置换不会实质上改变蛋白的功能特性。在两个或更多个氨基酸序列彼此差别在于保守置换的情况下,可以上调序列同一性百分比或同源性程度以校正置换的保守性质。进行这种调节的方法是本领域技术人员众所周知的(参见,例如,pearson等人,1994,特此通过引用并入本文)。
在一些情况下,可以使用“同工酶”,其实现相同的功能转化/反应,但其结构如此不同以至于它们通常被确定为不是“同源的”。
“保守氨基酸置换”是其中氨基酸残基被具有相似侧链的氨基酸残基替换的置换。具有类似侧链的氨基酸残基家族已经在本领域中定义。这些家族包括具有碱性侧链的氨基酸(例如,赖氨酸、精氨酸、组氨酸)、具有酸性侧链的氨基酸(例如,天冬氨酸、谷氨酸)、具有不带电荷的极性侧链的氨基酸(例如,甘氨酸、天冬酰胺、谷氨酰胺、丝氨酸、苏氨酸、酪氨酸、半胱氨酸)、具有非极性侧链的氨基酸(例如,丙氨酸、缬氨酸、亮氨酸、异亮氨酸、脯氨酸、苯丙氨酸、甲硫氨酸、色氨酸)、具有β-支化侧链的氨基酸(例如,苏氨酸、缬氨酸、异亮氨酸)和具有芳族侧链的氨基酸(例如,酪氨酸、苯丙氨酸、色氨酸、组氨酸)。以下六组各自含有对于彼此为保守置换的氨基酸:1)丝氨酸(s)、苏氨酸(t);2)天冬氨酸(d)、谷氨酸(e);3)天冬酰胺(n)、谷氨酰胺(q);4)精氨酸(r)、赖氨酸(k);5)异亮氨酸(i)、亮氨酸(l)、甲硫氨酸(m)、丙氨酸(a)、缬氨酸(v)和6)苯丙氨酸(f)、酪氨酸(y)、色氨酸(w)。
通常使用序列分析软件来测量多肽的序列同源性,其也可以被称作序列同一性百分比。参见,例如,威斯康辛州大学生物技术中心(universityofwisconsinbiotechnologycenter,910universityavenue,madison,wis.53705)遗传计算机组(geneticscomputergroup,gcg)的序列分析软件包。蛋白分析软件使用为各种置换、缺失和其它修饰(包括保守氨基酸置换)指定的同源性的量度来匹配相似的序列。例如,gcg含有程序诸如“gap”和“bestfit”,其可以与默认参数一起用来确定密切相关的多肽(诸如来自不同生物物种的同源多肽)之间或野生型蛋白和其突变蛋白之间的序列同源性或序列同一性。参见,例如,gcg6.1版。
将分子序列与含有来自不同生物体的大量序列的数据库进行对比而使用的典型算法是计算机程序blast(altschul,1990;gish,1993;madden,1996;altschul,1997;zhang,1997),特别是blastp或tblastn(altschul,1997)。用于blastp的典型参数是:期望值:10(默认);过滤器:seg(默认);开放缺口罚分(costtoextendagap):11(默认);延伸缺口罚分(costtoextendagap):1(默认);最大比对:100(默认);字长:11(默认);描述数目(no.ofdescriptions):100(默认);罚分矩阵:blowsum62。
当搜索含有来自大量不同生物体的序列的数据库时,通常对比氨基酸序列。可以通过本领域已知的除blastp之外的算法来测量使用氨基酸序列的数据库搜索。例如,可以使用fasta(gcg6.1版中的一个程序)对比多肽序列。fasta提供了查询序列和搜索序列之间的最佳重叠区域的比对和序列同一性百分比(pearson,1990,特此通过引用并入本文)。例如,使用fasta及其默认参数(字长2和pam250评分矩阵)可以确定氨基酸序列之间的序列同一性百分比,如在gcg6.1版中所提供,特此通过引用并入本文。
本公开内容提供了可用于产生用在体外系统中的重组微生物和蛋白的各种基因、同系物和变体的登录号和序列。应当理解,本文描述的同系物和变体是示例性的和非限制性的。使用各种数据库,包括例如可在万维网上访问的国家生物技术信息中心(ncbi),本领域技术人员可获得另外的同系物、变体和序列。
利用本文描述的序列和登录号来鉴定可用于或替代本文使用的任何多肽的同系物和同工酶完全是在本领域的技术水平内。实际上,本文提供的任一种序列的blast搜索将鉴定多个相关的同系物。
适合于培养和维持本文提供的重组微生物的培养条件是已知的(参见,例如,freshney的“cultureofanimalcells--amanualofbasictechnique”,wiley-liss,n.y.(1994),第三版)。熟练的技术人员将认识到,可以改变这样的条件以适应每种微生物的需求。
应当理解,可以修饰一系列微生物以包括适合于生产异戊二烯化的化合物或大麻素或大麻素前体的重组代谢途径的全部或部分。还理解,多种微生物可以充当编码适用于本文提供的重组微生物中的靶酶的遗传物质的“来源”。
如以前讨论的,描述本文中可用的分子生物学技术(包括载体、启动子的使用和许多其它相关主题)的通用教材包括berger和kimmel,guidetomolecularcloningtechniques,methodsinenzymology第152卷,(academicpress,inc.,sandiego,calif.)(“berger”);sambrook等人,molecularcloning--alaboratorymanual,第2版,第1-3卷,coldspringharborlaboratory,coldspringharbor,n.y.,1989(“sambrook”)和currentprotocolsinmolecularbiology,f.m.ausubel等人,编,currentprotocols,ajointventurebetweengreenepublishingassociates,inc.andjohnwiley&sons,inc.,(1999年增刊)(“ausubel”),它们中的每一篇通过引用整体并入本文。
足以指导技术人员进行体外扩增方法(包括聚合酶链式反应(pcr)、连接酶链式反应(lcr)、qβ-复制酶扩增和其它rna聚合酶介导的技术(例如,nasba)(例如,用于生产本公开内容的同源核酸))的方案的例子参见berger,sambrook,和ausubel,以及mullis等人(1987)美国专利号4,683,202;innis等人,编(1990)pcrprotocols:aguidetomethodsandapplications(academicpressinc.sandiego,calif.)(“innis”);arnheim和levinson(1990年10月1日)c&en36-47;thejournalofnihresearch(1991)3:81-94;kwoh等人(1989)proc.natl.acad.sci.usa86:1173;guatelli等人(1990)proc.nat'l.acad.sci.usa87:1874;lomell等人(1989)j.clin.chem35:1826;landegren等人(1988)science241:1077-1080;vanbrunt(1990)biotechnology8:291-294;wu和wallace(1989)gene4:560;barringer等人(1990)gene89:117;以及sooknanan和malek(1995)biotechnology13:563-564。
用于克隆体外扩增的核酸的改进方法描述于wallace等人,美国专利号5,426,039中。
通过pcr扩增大核酸的改进方法总结在cheng等人(1994)nature369:684-685和其中引用的参考文献中,其中产生了高达40kb的pcr扩增子。技术人员将明白,使用逆转录酶和聚合酶,基本上任何rna都可被转化为适合于限制性消化、pcr扩增和测序的双链dna。参见,例如,ausubel,sambrook和berger,都出处同上。
在以下实施例中举例说明了本发明,这些实施例以举例说明的方式提供且无意进行限制。
实施例
化学物质和试剂.酵母己糖激酶和谷氨酸棒杆菌(corynebacteriumglutamicum)过氧化氢酶购自sigmaaldrich。绿色气球菌丙酮酸氧化酶购自a.g.scientific。所有的辅因子和试剂都购自sigmaaldrich或thermofisherscientific,例外是购自santacruzbiotechnology的油橄榄醇酸和购自torontoresearchchemicals的divarinicacid。
酶的克隆和纯化.从idtdna购买nphb基因作为基因块,并使用gibsonassembly方法克隆到pet28(+)载体中。从基因组dna或质粒扩增剩余的酶,并使用相同的gibsonassembly方法克隆到pet28(+)中。将所有质粒转化到bl21(de3)gold中,并在含50μg/ml卡那霉素的lb培养基中表达酶。给1l培养物接种2ml在相同培养基中的饱和培养物,并在37℃生长至0.5-0.8的od600。用1mmiptg诱导培养物,并在18℃表达16小时。通过以2,500xg离心收获细胞,并重新悬浮于约20ml裂解缓冲液:50mmtris[ph8.0],150mmnacl,和10mm咪唑。使用emulsiflex仪器裂解细胞。通过以20,000xg离心将裂解物澄清,并将上清液在4℃分批结合1mlninta树脂30分钟。将该树脂转移至重力流动柱。将树脂用10柱体积的洗涤缓冲液(50mmtris[ph8.0],150mmnacl,和10mm咪唑)洗涤。然后用2柱体积的洗脱缓冲液(50mmtris[ph8.0],150mmnacl,250mm咪唑和30%(v/v)甘油)洗脱蛋白。使用液氮将酶在洗脱缓冲液中快速冷冻,并将酶储备液保存在-80℃。
pdh无细胞反应.pdh反应以两部分组装。首先,将辅因子和底物在一个试管中组合,并在另一个试管中组合酶。通过以200μl的终体积混合辅因子和酶来引发反应。最终的底物和辅因子浓度如下:500mm葡萄糖,1mm1,6果糖二磷酸,4mmatp,0.5mm2,3二磷酸甘油酸酯,0.5mmnad+,1.5mmcoa,1.5mmnadp+,0.5mmtpp,6mmmgcl2,10mmkcl,50mmtris[ph8.0]和20mm磷酸盐缓冲液[ph8.0],5mm谷胱甘肽和0.5-5mm1,6dhn。在24小时淬灭反应。
pdh活性测定.在几种芳族聚酮化合物存在下测定pdh的活性。媒介物对照是1%乙醇,并且将活性与没有芳族聚酮化合物的测定进行比较。最终反应体积为200μl,且含有2mmnad+、2mmcoa、1mmtpp、5mmmgcl2、5mmkcl、50mmtrisph8.0和5μl1.25mg/mlpdh。在96孔板中设置反应。加入芳族聚酮化合物至1mm的终浓度,并加入乙醇对照至1%(v/v)的终浓度。将板在室温温育10分钟,并用10μl100mm丙酮酸引发反应。使用m200波谱仪监测在340nm的吸光度10分钟。由于芳族分子在340nm处具有背景吸光度,因此使用反应混合物和芳族分子给反应建立空白,但不用丙酮酸引发反应,而是添加水。使用线性拟合的初始斜率确定初始速率。使用beer定律和6.22x103m-1cm-1的消光系数,计算每单位时间产生的nadh的量。一式三份进行反应,并计算平均值和标准误差。
pyox/pta无细胞反应.pyox/pta反应以两部分组装。首先,将辅因子和底物在一个试管中组合,并在另一个试管中组合酶。在200μl反应中的最终辅因子和底物浓度如下:500mm葡萄糖,1mm1,6果糖二磷酸,4mmatp,0.5mm2,3二磷酸甘油酸酯,0.5mmnad+,1.5mmcoa,3mmnadp+,0.5mmtpp,6mmmgcl2,10mmkcl,50mmtrisph8.0和50mm磷酸盐缓冲液[ph8.0]。在表3中详细列出了添加到每个反应中的酶的量。混合辅因子和酶以引发反应,并在顶部添加500μl壬烷覆盖物。将反应物在室温在凝胶振荡器上轻轻振荡温育。
对于1,6dhn/5-p-1,6dhn:当芳族底物是变化的组分时,将0.5-5mm芳族底物加入反应中,并在24小时淬灭反应。当时间是变化的组分时,加入5mm1,6dhn,并在约12、24、48和72小时淬灭单独的反应。
对于油橄榄醇酯/cbga:大麻素途径的优化显示,用较少的葡萄糖可达到相同的滴度,因此葡萄糖浓度降至150mm。此外,将nadp+浓度增加到6mm并将atp浓度减少到1mm导致更高的cbga滴度。油橄榄醇酯浓度设定为5mm。添加到反应中的nphb的量是可变的。在图2c中显示的数据利用1.5mg/mlnphb,并在约4、8、14、24、48、72和96小时淬灭反应。在图4a中显示的数据是使用0.5mg/mlwtnphb和m23获得,并且在约6、9、12、24、48、72和96小时淬灭反应。
对于divarinicacid/cbgva:条件与上述一般方法非常相似,不同之处在于使用了150mm葡萄糖、1mmatp和6mmnadp+,并在约6、9、12、24和48小时淬灭反应。此外,异戊二烯基转移酶的终浓度为1mg/ml,并且我们用芹菜配基、黄豆苷元、染料木黄酮、柚皮素和白藜芦醇测试了atapt、novq和nphb。我们还用油橄榄醇、油橄榄醇酯和1,6dhn测试了nphb。在24小时淬灭反应。
淬灭反应.为了淬灭反应,将水层和有机层转移至1.5ml微量离心管。用200μl乙酸乙酯洗涤反应小瓶,然后将其与微量离心管中的反应物合并。将样品涡旋5-10秒,且然后以13,000rpm离心3分钟。除去有机层,并将剩余的水层用200μl乙酸乙酯再萃取两次。对于每个样品,将有机萃取物合并,且然后使用真空离心机蒸发。将样品重新溶解在甲醇中用于hplc分析。
对于油橄榄醇酯/cbga:由于观察到蛋白沉淀,在存在0.12g尿素(固体)的情况下提取了图4a中所示的cbga反应物,以促进cbga的提取。这对于图2c中的wtnphbcbga数据来说是不必要的,因为蛋白不沉淀。
产物的定量.使用thermoultimate3000hplc在c18柱(4.6×100mm)上通过反相色谱法分级分离反应物。将柱隔室温度设定为40℃,并且流速为1ml/min。使用水+0.1%tfa(溶剂a)和乙腈+0.1%tfa(溶剂b)作为流动相,用梯度洗脱分离化合物。将溶剂b保持在20%持续第1分钟。然后在4分钟内将溶剂b增加到95%b,且然后将95%b保持3分钟。然后将柱重新平衡至20%b持续3分钟,总运行时间为11分钟。
使用从由sigmaaldrich购买的分析标准品所衍生出的外部校正曲线定量大麻素(cbga、cbda和cbdva)。5-p-1,6-dhn和cbgva核磁共振(nmr)样品用于生成外部校正曲线,因为没有可靠标准品可用。将已知浓度的标准品溶解在水中,且然后使用上面详述的方法提取。
在没有可靠标准品的情况下定量异戊二烯基产物.由于缺乏异戊二烯基产物异戊二烯基-芹菜配基、异戊二烯基-黄豆苷元、异戊二烯基-柚皮素、异戊二烯基-染料木黄酮、异戊二烯基-白藜芦醇和异戊二烯基-橄榄醇的可靠标准品,因此基于底物消耗来定量异戊二烯基产物。为了产生标准曲线,将每种芳族底物的系列稀释液进行反应混合,但是为了防止产物形成,异戊二烯基-转移酶被省去。与标准曲线相比,使用液相色谱法-质谱法定量被反应消耗的底物的量。
在由masslynx4.1软件(waterscorporation,milford,ma)控制的waterslct-premierxe飞行时间仪器上进行电喷射电离飞行时间测量。该仪器配备有以电喷雾模式操作的多模式电离源。将亮氨酸脑啡肽(sigmachemical,l9133)的溶液用于lock-spray以获得准确的质量测量值。在watersacquityuplc系统上使用直接环注射注入样品。使用acquitybehc181.7μm柱(50×2.1mm)在watersacquityuplc系统上分离样品,并用30-95%溶剂b的梯度历时10min(溶剂a:水,溶剂b:乙腈,二者含有0.2%甲酸(vol/vol))洗脱。从300-2000da的质量记录质谱图。
nmr光谱法.使用nmr光谱法鉴定异戊二烯基产物,并定量5-p-1,6-dhn。
对于1,6dhn/5-p-1,6dhn:使用pyox/pta无细胞系统生产异戊二烯基-dhn。合并200μl反应物,并用等量壬烷萃取3次,且然后蒸发壬烷。将反应的产物悬浮于500μl氘代甲醇(cd3od)中,以2mm1,3,5-三甲氧基苯(tmb)作为内部标准品。在av400brukernmr谱仪上收集波谱。参考内部tmb标准品测定样品中异戊二烯化的化合物的量。将来自6.05ppm的tmb(3h,s)的质子信号与对应于7.27ppm的5-p-1,6-dhn(1h,d)的芳族质子进行比较。
对于divarinicacid/cbgva:还使用nmr来鉴定以divarinicacid作为芳族底物的酶促系统的产物。如上详述建立pyox/pta系统,并将在24小时淬灭反应。如上详述提取反应,并在hplc上分析。在6.7分钟时出现一个新的主峰,其预计为异戊二烯化的divarinicacid。纯化hplc峰,除去溶剂,并将纯组分重新溶解在600μlcd3od中。将使用av500brukernmr谱仪收集的质子谱图与shoyama等人发表的cbgva的质子谱图进行比较,以确认cbgva是主要产物。基于shoyama等人的论文,bohlman等人的论文,结论是,divarinicacid的异戊二烯化发生在divarinicacid的c3碳处。
修饰nphb的结合口袋以接受油橄榄醇酯的rosetta设计.将油橄榄醇酯放在nphb的活性位点中在六个不同的起始位置,所述位置表示为表4中的油橄榄醇酯p1-6。对每个油橄榄醇酯位置运行rosetta5次,总共30次设计。表4列出了在每种设计中预测的突变。对于每个油橄榄醇酯位置,选择一组共有突变(即,最常选择的残基)以进一步评价:共有组a至f(表4)。然后评价每个rossetta建议的突变的相对重要性。对于每个共有组,将突变设置回wt残基,一次一个,并使用rosetta计算能量评分的变化(参见表5)。引起最大能量变化的那些突变被认为是最重要的突变体,以包括在用于实验测试的文库中。
表4
表5
为了建模油橄榄醇酸,使用来自5b09晶体结构的油橄榄醇酯的4mx.sdf3-d结构,并使用openbabel2.3.1在假定ph7的情况下将氢原子添加至该结构。使用生物化学文库(bcl)分子为油橄榄醇酸生成了旋转异构体文库:使用pdb文库生成了conformergenerator3.5。最后,在使用rosetta3.7版本中的脚本main/source/python/public/molfile_to_params.py生成由rosetta读出的参数文件之前,将芳族键手动注释到文件中。使用来自1zb6晶体结构的gst.sdf文件,在没有旋转异构体文库的情况下生成了香叶基s-巯基二磷酸酯(gst)的参数文件。然后将油橄榄醇酸分子手工放置进nphb与gst和dhn的共晶体结构(1zb6)中,其中使用pymol脱除dhn和结晶水。将油橄榄醇酸放置在活性位点的6个不同位置,其中油橄榄醇酯芳族环的平面平行于gst烷基尾巴,且期望的异戊二烯化位点与最终的碳阳离子相距3.7埃,这反映了dhn在1zb6晶体结构中的位置。在rosetta设计过程中,允许残基49、162、213、224、232、233、234、271、286和288是任何氨基酸,而其它侧链则保持在固定位置,且主链固定。设计的残基与油橄榄醇酯直接接触,而不与gst直接接触。来自rosetta3.7版本的固定主链脚本main/source/bin/fixbb.static.linuxgccrelease用所有可能的旋转异构体(-ex4)运行,使用输入侧链(-use_input_sc)、设计后最小化的侧链(minimize_sidechains)、线性记忆节点交互图(-linmem_ig10)以及有和没有配体加权得分函数(-score:weightsligand)。从相同的起点,使用-nstruct输入将每个设计运行5次。从rosetta建议的一组突变中,选择发生频率最高且对rosetta评分函数贡献最大的突变,从而创建了22个突变体的文库用于实验测试。
初始nphb突变体文库筛选.为了筛选初始文库,进行了小规模表达和纯化。给25mllb培养基接种25μl带有nphb表达质粒的bl21de3gold的饱和培养物。将培养物在37℃温育直至od600达到0.4-0.6。通过添加1mmiptg来诱导nphb构建体的表达,然后在18℃温育18小时。通过以2500xg离心收获细胞。将沉淀重新悬浮于500μl裂解缓冲液:50mm[trisph8.0],150mmnacl,和5mm咪唑,并通过声处理裂解。通过在4℃以20,000xg离心10分钟来澄清细胞裂解物,并将上清液在4℃与50μlninta树脂一起温育。使用96-孔旋转柱板纯化nphb构建体。将上清液/树脂上样至柱,并以500xg离心2分钟。然后加入500μl裂解缓冲液,并将板再次以500xg离心1分钟。使用200μl洗脱缓冲液(50mmtris[ph8.0],150mmnacl,250mm咪唑和30%(v/v)甘油)洗脱蛋白。
在以下条件下测定酶:2.5mm香叶基焦磷酸酯,5mm油橄榄醇酯,5mmmgcl2,50mmtrisph8.0,约0.1mg/mlnphb突变体,最终体积为100μl。首先使用洗脱缓冲液将所有酶稀释至0.5mg/ml,使得在每个反应中咪唑的终浓度相同。将反应在室温温育12小时,然后用100μl乙酸乙酯萃取3次。为每个反应合并有机萃取物,并使用真空离心机除去溶剂。将样品重新溶解在100μl甲醇中,并进行hplc分析。
聚焦nphb突变体文库筛选.对于聚焦文库,进行如上所述的1l规模的nphb构建体表达和纯化。在以下条件下测定酶:2.5mmgpp,5mm油橄榄醇酯,5mmmgcl2,50mmtrisph8.0和约1mg/mlnphb酶,最终体积为100μl。将反应在室温温育1小时。在80μl乙腈中淬灭40μl每个反应。将样品以13,000rpm离心5分钟,以除去沉淀的蛋白。如上所述,使用hplc分析上清液。
酶动力学参数.在以下条件下设置反应:50mmtris[ph8.0],2.5mmgpp,5mmmgcl2,约27μm酶,和在0.1mm至6mm变化的油橄榄醇酯或divarinicacid,最终体积为200μl。以下面详述的时间间隔,在80μl乙腈+0.1%tfa中淬灭40μl反应。将反应物以13,000-16,060xg离心5分钟以使蛋白沉淀,并使用上文详述的hplc方法分析上清液。绘制初始速率相对于底物浓度的图,并与michaelis-menten方程拟合以确定动力学参数kcat和km(originpro)。一式三份地执行每条michaelis-menten曲线。报道了动力学参数的平均值和标准偏差。
对于油橄榄醇酯/cbga:对于wt、m1、m10和m30,时程为3、6、9和12分钟。对于突变体25,在1、2、4和8分钟淬灭反应,且对于m31,在1、2、4和6分钟淬灭反应。
对于divarinicacid/cbgva:对于m31,时程为0.5、1、1.5和2分钟。对于m23,时程为5、10、15和20分钟,且对于wtnphb,时程为8、16、24和32分钟。突变体的酶浓度为约27μm,且wtnphb的浓度为约35μm。
来自wtnphb和m23的异构体概况的gc-ms表征.将样品溶解在200μl乙酸乙酯中。使用agilentmodel7693自动采样器、7890b气相色谱仪和7250q-tof质量选择性检测器(以电子电离模式)进行gc-ms测量。样品注射以分流模式进行,其中入口温度设置为280℃。在尺寸为30mx250μmx0.25μm的agilenthp5-ms柱上进行分离。以恒定流模式,将超高纯等级he(airgas)用作载气,流量设置为1.1ml/min。将初始恒温箱温度设置为120℃持续1分钟,然后以20℃/min的速度升至300℃的最终温度并保持4分钟。使用了3.0分钟的溶剂延迟。el能量设置为15ev。msd设置为扫描50-500m/z范围。使用masshunter采集和定性分析软件(agilent)进行数据收集和分析。
由于gc入口的温度升高,cbga经历了自发的脱羧,如radwan等人所述,导致在316m/z的m+离子。对应于cbga标准品的316m/z离子的保留时间为10.48分钟。
用于从溶液中萃取cbga的壬烷-流动系统.如上所详述建立了pyox/pta反应。将500μl壬烷覆盖物添加到在2ml玻璃小瓶中的反应物中,该玻璃小瓶覆盖有2层可呼吸的细胞培养膜。将两个针插入15mlfalcon管中的约750μl标记和3.5ml标记处。将管道连接器的路厄锁连接到针头,并将viton管道连接到路厄锁的另一端。将针通过路厄锁连接器连接到管道的另一端,并穿过网状覆盖物插入,所以它们仅接触壬烷层且不接触反应物。将2mltris缓冲液[ph8.5]添加到15ml锥形管中,并添加6ml壬烷。使用蠕动泵将壬烷泵送通过系统,使得壬烷从反应顶部流过缓冲溶液。将壬烷泵入蓄池,分离到15ml锥形管的顶层。将来自15ml锥形管的顶部的壬烷泵入反应小瓶的顶部。这基本上稀释了整个系统中的cbga,从而驱动cbga扩散到壬烷层中并扩散出反应。
克隆cbdas.从针对巴斯德毕赤酵母(pichiapastoris)优化的idt密码子订购了cbdas的基因块。通过从蛋白序列的第28个残基(npren…)到蛋白末端进行pcr扩增,除去信号序列,其突出端与ppiczα载体相容。使用gibson克隆方法将pcr产物克隆到用ecori和xbai消化的ppiczα载体中。将组装反应的产物转化进bl21gold(de3)细胞,分离具有正确序列的克隆。将该质粒用pmei消化2小时,且然后使用qiagenpcr纯化方案纯化。使用电穿孔将质粒转化到巴斯德毕赤酵母x33中。在电穿孔以后,立即将细胞在1ml冷的1m山梨醇和1mlypd培养基中在没有摇动下温育2小时。将细胞铺板在具有500μg/mlzeocin的ypds平板上。关于cbdas基因在aox1启动子和终止子之间的存在,使用pcr筛选菌落。为了筛选,将菌落重新悬浮于15μl无菌水中,并将5μl重新悬浮的菌落转移进含0.2%sds的pcr管中。将样品在99℃加热10分钟,且然后将1μl用作pcr的模板。关于cbdas的表达,筛选具有阳性菌落pcr命中的六个菌落。
cbdas表达测试.使六个菌落在30℃生长过夜以获得饱和培养物。将过夜培养物用于接种在bmgy培养基中的25ml培养物,并生长至约2的od。通过以2,000xg离心10分钟来收获细胞。将细胞沉淀物重新悬浮在90mlbmmy培养基中,并在30℃温育5天。每天,取出1ml培养物用于sds-page分析,并添加500μl甲醇。在第3天,针对cbdas活性筛选培养物。测定条件如下:100μl200mm柠檬酸盐缓冲液,100μmcbga,5mmmgcl2,5mmkcl,1mmfad和50μl表达培养基,最终体积为200μl。将反应物在室温温育过夜,且然后用200μl乙酸乙酯萃取3次。为每个样品合并乙酸乙酯萃取液,并用真空离心机除去。将样品重新悬浮于200μl甲醇中,并通过hplc分析。所有克隆均产生活性cbdas。
收集来自三个克隆(总共约300ml)的培养物以获得cbdas活性。通过在4℃以约3,000xg离心20分钟,使细胞沉淀。然后使上清液穿过0.22μm过滤器。浓缩培养基,并使用来自millipore的50,000mwco蛋白浓缩器将缓冲液更换为100mm柠檬酸盐缓冲液ph5.0。使用bradford测定法确定培养基浓缩物中的总蛋白为0.4mg/ml,总产率为约5mg/l总蛋白。
cbdva和cbda的生产.为了将前体cbga和cbgva分别转化为cbda和cbgva,用cbdas合酶建立了二级反应。
对于cbga/cbda:如上所详述建立了pyox/pta酶促系统以生产cbga。24小时后,将200μl来自cbga反应的壬烷覆盖物转移至cbdas反应容器。在水层中:50mmhepes[ph7.0],5mmmgcl2,5mmkcl,25μmfad,0.1mg/mlcbdas浓缩物。将反应物在30℃在轻轻摇动下温育。在12、24、48、72和96小时淬灭反应。
对于cbgva/cbdva:将hplc纯化的cbgva转化为cbdva。最终反应体积为200μl,含有50mmhepes[ph7.0]、5mmmgcl2、5mmkcl、25μmfad和0.1mg/ml(总蛋白)的cbdas浓缩物。添加200μl壬烷覆盖物,并在30℃在轻轻摇动下温育反应。在约24、48、72和96小时淬灭反应。
matb活性测定.在有oa和da存在下使用偶联酶促测定来确定来自r.palustris的丙二酰基辅酶a合成酶(matb)(参见,例如,seqidno:82-83)的活性。反应条件为:2.5mm丙二酸,2mmatp,1mmcoa,2.5mm磷酸烯醇丙酮酸(pep),1mmnadh,5mmmgcl2,10mmkcl,0.35mg/mladk,0.75μg/mlmatb,1.6单位的pk和2.5单位的ldh,和50mmtris[ph8.0]。通过忽略底物(丙二酸)来控制背景atp酶活性,并将1%乙醇、250μm或5mmoa或5mmda添加到其余反应中。通过使用m2spectramax监测由于nadh消耗引起的在340nm的吸光度的降低,确定matb的活性。为确保matb在5mmoa或da是限制性的,将matb加倍至1.5μg/ml。反应速率增加了一倍,表明matb是系统中的限制性组分。将在5mmoa和5mmda的nadh消耗率针对1%乙醇对照归一化。
aae3活性测定.在有oa和da存在下,使用与上述相似的偶联酶促测定来确定酰基活化酶3(aae3)(参见,例如,seqidno:70-71和同系物-seqidno:72-75)的活性。条件与matb测定相同,具有以下修改:添加2.5mm己酸代替丙二酸,并添加15μg/mlaae3代替matb。为了确保aae3是限制性的,在有5mmoa或da存在下使aae3加倍。反应速率加倍,表明aae3是限制性的。
adk活性测定.在有oa和da存在下,使用偶联酶促测定来确定腺苷酸激酶(adk)(参见,例如,seqidno:)的活性。条件与matb测定相同,具有以下修改:添加2mmamp代替丙二酸,不添加coa,并添加0.001mg/mladk。为了确保adk在5mmoa和da下是限制性试剂,将adk的量加倍。速率的2倍增加表明adk是限制因素。
cpk活性测定.在有oa或da存在下使用偶联酶促测定来确定肌酸激酶(cpk)的活性。反应条件为:5mm磷酸肌酸,2mmadp,5mm葡萄糖,2mmnadp+,5mmmgcl2,5mmkcl,0.3mg/mlzwf,0.1mg/mlschex和0.08单位cpk。阳性对照反应含有1%乙醇,并将5mmoa或da添加到其余反应中。监测nadph在340nm处的吸光度。为了确保cpk是限制性的,在5mmoa和5mmda将其加倍。得到的速率加倍,其表明,即使在高oa和da,cpk也是限制性的。
ols活性测定.通过设置以下条件来测定油橄榄醇合酶(ols)(参见,例如,seqidno:76-77):200μm丙二酰基辅酶a,100μm己酰基辅酶a,0.65mg/mloas,在50mm柠檬酸盐缓冲液ph5.5或50mmtris缓冲液ph8.0中。通过加入oas来引发反应,且然后在30分钟通过向50μl反应物中添加150μl甲醇来淬灭反应。将样品以约16,000xg离心2分钟以沉淀蛋白。使用hplc分析上清液。
对于抑制实验,将条件改变为:1mm丙二酰基辅酶a,400μm己酰基辅酶a,在50mm柠檬酸盐缓冲液ph5.5中,最终体积为200μl。将1%乙醇、250μmoa或1mmda添加到反应中,且然后通过添加0.65mg/mlols来引发反应。将50μl等分试样在2、4、6和8分钟在150μl甲醇中淬灭。将反应物短暂涡旋并以16,000xg离心2分钟以沉淀蛋白。通过hplc分析上清液。将htal、pdal和油橄榄醇的原始峰面积相加,并相对于时间作图以确定速率。将补充了oa的反应和补充了da的反应的速率针对乙醇对照归一化。
ols/oac活性测定.为了产生oa,使用与上面指定的相同的ols条件,但是将油橄榄醇酸环化酶(oac)(参见,例如,seqidno:78-79)以0.6mg/ml加入到反应中。将反应淬灭,并以与ols测定相同的方式进行分析。将乙酰基磷酸酯和bsa分别以5mm-40mmacp和10-30mg/mlbsa终浓度添加到测定中。
完整途径设置.在该研究中使用的酶和终浓度(mg/ml)可以在表6(对于matb路径)和表7(对于mdca路径)中找到。对于matb路径,以以下浓度添加辅因子:150mm葡萄糖,1mm果糖二磷酸,2mmatp,0.25mmnad+,3mmnadp+,2mmcoa,0.25mm2,3-二磷酸甘油酸酯,6mmmgcl2,10mmkcl,0.5mm硫胺素焦磷酸盐,50mm磷酸盐ph8.0,5mm己酸,15mm丙二酸,5mm磷酸肌酸,和50mmtris,ph8.0。通过添加表6中列出的酶来引发反应。将反应在室温温育过夜,并将反应淬灭并用200μl乙酸乙酯萃取3次。使用真空离心机除去乙酸乙酯。将样品溶解在200μl甲醇中,并使用hplc分析。
表6:在完整大麻素matb途径中使用的酶以及最终酶浓度
表7:在完整大麻素mdca途径中使用的酶以及最终酶浓度
mdca路径的酶可以在表7中找到。在上面指定的相同辅因子条件下设置mdca反应,但有以下变化:3mmatp,0.25mmamp,25mm磷酸肌酸且无tris缓冲液。
在图5a-b中提供了matb和mdca途径的途径。
已经描述了本发明的某些实施方案。应该理解,在不脱离本发明的精神和范围的情况下可以做出各种修改。其它实施方案在下述权利要求的范围内。
序列表
<110>加利福尼亚大学董事会
<120>用于生产大麻素和其它异戊二烯化的化合物的生物合成平台
<130>00011-089wo1
<140>尚未指定
<141>2019-08-01
<150>us62/713,348
<151>2018-08-01
<160>83
<170>patentin3.5版
<210>1
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm1
<400>1
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>2
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm2
<400>2
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>3
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm3
<400>3
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserhisservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>4
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm4
<400>4
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>5
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm5
<400>5
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalserphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>6
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm6
<400>6
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalasnphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalasertyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>7
<211>327
<212>prt
<213>人工的
<220>
<223>nphbm7
<400>7
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalserphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>8
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm8
<400>8
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalthrphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>9
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm9
<400>9
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalthrserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>10
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm10
<400>10
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>11
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm11
<400>11
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalglyphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>12
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm12
<400>12
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalthrserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>13
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm13
<400>13
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalasnphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalasertyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>14
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm14
<400>14
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserglyservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalthrserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>15
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm15
<400>15
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>16
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm16
<400>16
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>17
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm17
<400>17
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalthrphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserglyservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>18
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm18
<400>18
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalserphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuasntyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>19
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm19
<400>19
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalserphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuasntyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>20
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm20
<400>20
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalthrphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserglyservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuhistyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>21
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm21
<400>21
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalserphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserasnservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalthrserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuasntyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>22
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm22
<400>22
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalthrphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserglyservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalthrserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuhistyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuglyalaasntyrhisilethraspvalglnargglyileleulys
305310315320
alapheaspserleugluasp
325
<210>23
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm23
<400>23
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>24
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm24
<400>24
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>25
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm25
<400>25
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserhisservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralaalatyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>26
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm27
<400>26
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucysphealavalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralavaltyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>27
<211>327
<212>prt
<213>人工序列
<220>
<223>nphbm28
<400>27
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheservalileserasn
245250255
aspprothrleuvalproserseraspgluglyaspileglulysphe
260265270
hisasntyralathrlysalaprotyralatyrvalglyglulysarg
275280285
thrleuvaltyrglyleuthrleuserprolysgluglutyrtyrlys
290295300
leuseralavaltyrhisilethraspvalglnargglyleuleulys
305310315320
alapheaspserleugluasp
325
<210>28
<211>328
<212>prt
<213>人工序列
<220>
<223>nphbm30
<400>28
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheseralavalileser
245250255
asnaspprothrleuvalproserseraspgluglyaspileglulys
260265270
phehisasntyralathrlysalaprotyralatyrvalglyglulys
275280285
argthrleuvaltyrglyleuthrleuserprolysgluglutyrtyr
290295300
lysleuglyalaalatyrhisilethraspvalglnargglyleuleu
305310315320
lysalapheaspserleugluasp
325
<210>29
<211>328
<212>prt
<213>人工序列
<220>
<223>nphbm31
<400>29
metglyserserhishishishishishisserserglyleuvalpro
151015
argglyserhismetserglualaalaaspvalgluargvaltyrala
202530
alametgluglualaalaglyleuleuglyvalalacysalaargasp
354045
lysiletyrproleuleuserthrpheglnaspthrleuvalglugly
505560
glyservalvalvalphesermetalaserglyarghisserthrglu
65707580
leuasppheserileservalprothrserhisglyaspprotyrala
859095
thrvalvalglulysglyleupheproalathrglyhisprovalasp
100105110
aspleuleualaaspthrglnlyshisleuprovalsermetpheala
115120125
ileaspglygluvalthrglyglyphelyslysthrtyralaphephe
130135140
prothraspasnmetproglyvalalagluleuseralaileproser
145150155160
metproproalavalalagluasnalagluleuphealaargtyrgly
165170175
leuasplysvalglnmetthrsermetasptyrlyslysargglnval
180185190
asnleutyrphesergluleuseralaglnthrleuglualagluser
195200205
valleualaleuvalarggluleuglyleuhisvalproasngluleu
210215220
glyleulysphecyslysargserpheservaltyrprothrleuasn
225230235240
trpgluthrglylysileaspargleucyspheseralavalileser
245250255
asnaspprothrleuvalproserseraspgluglyaspileglulys
260265270
phehisasntyralathrlysalaprotyralatyrvalglyglulys
275280285
argthrleuvaltyrglyleuthrleuserprolysgluglutyrtyr
290295300
lysleuglyalavaltyrhisilethraspvalglnargglyleuleu
305310315320
lysalapheaspserleugluasp
325
<210>30
<211>307
<212>prt
<213>链霉菌属
<400>30
metserglualaalaaspvalgluargvaltyralaalametgluglu
151015
alaalaglyleuleuglyvalalacysalaargasplysiletyrpro
202530
leuleuserthrpheglnaspthrleuvalgluglyglyservalval
354045
valphesermetalaserglyarghisserthrgluleuasppheser
505560
ileservalprothrserhisglyaspprotyralathrvalvalglu
65707580
lysglyleupheproalathrglyhisprovalaspaspleuleuala
859095
aspthrglnlyshisleuprovalsermetphealaileaspglyglu
100105110
valthrglyglyphelyslysthrtyralaphepheprothraspasn
115120125
metproglyvalalagluleuseralaileprosermetproproala
130135140
valalagluasnalagluleuphealaargtyrglyleuasplysval
145150155160
glnmetthrsermetasptyrlyslysargglnvalasnleutyrphe
165170175
sergluleuseralaglnthrleuglualagluservalleualaleu
180185190
valarggluleuglyleuhisvalproasngluleuglyleulysphe
195200205
cyslysargserpheservaltyrprothrleuasntrpgluthrgly
210215220
lysileaspargleucysphealavalileserasnaspprothrleu
225230235240
valproserseraspgluglyaspileglulysphehisasntyrala
245250255
thrlysalaprotyralatyrvalglyglulysargthrleuvaltyr
260265270
glyleuthrleuserprolysgluglutyrtyrlysleuglyalatyr
275280285
tyrhisilethraspvalglnargglyleuleulysalapheaspser
290295300
leugluasp
305
<210>31
<211>449
<212>prt
<213>嗜热脱氮土壤芽孢杆菌
<400>31
metthrhisileargpheasptyrserlysalaleualaphephegly
151015
gluhisgluleuthrtyrleuargaspalavallysvalalahishis
202530
serleuhisglulysthrglyvalglyasnasppheleuglytrpleu
354045
asptrpprovalasntyrasplysglugluphealaargilelysgln
505560
alaalalyslysileglnseraspseraspvalleuleuvalilegly
65707580
ileglyglysertyrleuglyalaargalaalaileglumetleuhis
859095
hisserphetyrasnalaleuprolysglulysargserthrprogln
100105110
ileilephevalglyasnasnileserserthrtyrmetlysaspval
115120125
ileasppheleugluglylysasppheserileasnvalileserlys
130135140
serglythrthrthrgluproalailealapheargilephearglys
145150155160
leuleugluasplystyrglylysgluglualaargargargiletyr
165170175
alathrthraspargalaargglyalaleuargthrleualaaspglu
180185190
gluglytyrgluthrphevalileproaspaspileglyglyargtyr
195200205
servalleuthralavalglyleuleuproilealaalaserglyala
210215220
aspileaspalametmetgluglyalaalalysalaarggluaspphe
225230235240
serargsergluleuglugluasnalaalatyrglntyralaalaile
245250255
argasnileleutyrasnlysglylysthrilegluleuleuvalasn
260265270
tyrgluproalaleuhistyrphealaglutrptrplysglnleuphe
275280285
glyglusergluglylysaspglnlysglyiletyrproalaserala
290295300
asppheserthraspleuhisserleuglyglntyrileglnglugly
305310315320
argargaspleuphegluthrvalleulysleuglugluproarghis
325330335
gluleuvalileglualaglugluseraspleuaspglyleuasntyr
340345350
leualaglyglnthrvalaspphevalasnthrlysalapheglugly
355360365
thrleuleualahisthraspglyglyvalproasnleuvalvalthr
370375380
leuprolysleuaspglutyrthrpheglytyrleuvaltyrphephe
385390395400
glulysalacysalametserglytyrleuleuglyvalasnprophe
405410415
aspglnproglyvalglualatyrlyslysasnmetphealaleuleu
420425430
glylysproglytyrglugluleulysaspgluleuglulysargleu
435440445
lys
<210>32
<211>319
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>32
metlysargileglyvalleuthrserglyglyaspserproglymet
151015
asnalaalaileargservalvalarglysalailetyrhisglyval
202530
gluvaltyrglyvaltyrhisglytyralaglyleuilealaglyasn
354045
ilelyslysleugluvalglyaspvalglyaspileilehisarggly
505560
glythrileleutyrthralaargcysprogluphelysthrgluglu
65707580
glyglnlyslysglyilegluglnleulyslyshisglyileglugly
859095
leuvalvalileglyglyaspglysertyrglnglyalalyslysleu
100105110
thrgluhisglypheprocysvalglyvalproglythrileaspasn
115120125
aspileproglythraspphethrileglypheaspthralaleuasn
130135140
thrvalileaspalaileasplysileargaspthralathrserhis
145150155160
gluargthrtyrvalilegluvalmetglyarghisalaglyaspile
165170175
alaleutrpserglyleualaglyglyalagluthrileleuilepro
180185190
glualaasptyraspmetasnaspvalilealaargleulysarggly
195200205
hisgluargglylyslyshisserileileilevalalagluglyval
210215220
glyserglyvalasppheglyargglnileglnglualathrglyphe
225230235240
gluthrargvalthrvalleuglyhisvalglnargglyglyserpro
245250255
thralapheaspargvalleualaserargleuglyalaargalaval
260265270
gluleuleuleugluglylysglyglyargcysvalglyileglnasn
275280285
asnglnleuvalasphisaspilealaglualaleualaasnlyshis
290295300
thrileaspglnargmettyralaleuserlysgluleuserile
305310315
<210>33
<211>309
<212>prt
<213>大肠杆菌
<400>33
metvalargiletyrthrleuthrleualaproserleuaspserala
151015
thrilethrproglniletyrprogluglylysleuargcysthrala
202530
provalphegluproglyglyglyglyileasnvalalaargalaile
354045
alahisleuglyglyseralathralailepheproalaglyglyala
505560
thrglygluhisleuvalserleuleualaaspgluasnvalproval
65707580
alathrvalglualalysasptrpthrargglnasnleuhisvalhis
859095
valglualaserglygluglntyrargphevalmetproglyalaala
100105110
leuasngluaspglupheargglnleuglugluglnvalleugluile
115120125
gluserglyalaileleuvalileserglyserleuproproglyval
130135140
lysleuglulysleuthrglnleuileseralaalaglnlysglngly
145150155160
ileargcysilevalaspserserglyglualaleuseralaalaleu
165170175
alaileglyasnilegluleuvallysproasnglnlysgluleuser
180185190
alaleuvalasnarggluleuthrglnproaspaspvalarglysala
195200205
alaglngluilevalasnserglylysalalysargvalvalvalser
210215220
leuglyproglnglyalaleuglyvalaspsergluasncysilegln
225230235240
valvalproproprovallysserglnserthrvalglyalaglyasp
245250255
sermetvalglyalametthrleulysleualagluasnalaserleu
260265270
gluglumetvalargpheglyvalalaalaglyseralaalathrleu
275280285
asnglnglythrargleucysserhisaspaspthrglnlysiletyr
290295300
alatyrleuserarg
305
<210>34
<211>319
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>34
metlysargileglyvalleuthrserglyglyaspserproglymet
151015
asnalaalaileargservalvalarglysalailetyrhisglyval
202530
gluvaltyrglyvaltyrhisglytyralaglyleuilealaglyasn
354045
ilelyslysleugluvalglyaspvalglyaspileilehisarggly
505560
glythrileleutyrthralaargcysprogluphelysthrgluglu
65707580
glyglnlyslysglyilegluglnleulyslyshisglyileglugly
859095
leuvalvalileglyglyaspglysertyrglnglyalalyslysleu
100105110
thrgluhisglypheprocysvalglyvalproglythrileaspasn
115120125
aspileproglythraspphethrileglypheaspthralaleuasn
130135140
thrvalileaspalaileasplysileargaspthralathrserhis
145150155160
gluargthrtyrvalilegluvalmetglyarghisalaglyaspile
165170175
alaleutrpserglyleualaglyglyalagluthrileleuilepro
180185190
glualaasptyraspmetasnaspvalilealaargleulysarggly
195200205
hisglualaglylyslyshisserileileilevalalagluglyval
210215220
glyserglyvalasppheglyargglnileglnglualathrglyphe
225230235240
gluthrargvalthrvalleuglyhisvalglnargglyglyserpro
245250255
thralapheaspargvalleualaserargleuglyalaargalaval
260265270
gluleuleuleugluglylysglyglyargcysvalglyileglnasn
275280285
asnglnleuvalasphisaspilealaglualaleualaasnlyshis
290295300
thrileaspglnargmettyralaleuserlysgluleuserile
305310315
<210>35
<211>359
<212>prt
<213>大肠杆菌
<400>35
metserlysilepheaspphevallysproglyvalilethrglyasp
151015
aspvalglnlysvalpheglnvalalalysgluasnasnphealaleu
202530
proalavalasncysvalglythraspserileasnalavalleuglu
354045
thralaalalysvallysalaprovalilevalglnpheserasngly
505560
glyalaserpheilealaglylysglyvallysseraspvalprogln
65707580
glyalaalaileleuglyalaileserglyalahishisvalhisgln
859095
metalagluhistyrglyvalprovalileleuhisthrasphiscys
100105110
alalyslysleuleuprotrpileaspglyleuleuaspalaglyglu
115120125
lyshisphealaalathrglylysproleupheserserhismetile
130135140
aspleuserglugluserleuglngluasnilegluilecysserlys
145150155160
tyrleugluargmetserlysileglymetthrleugluilegluleu
165170175
glycysthrglyglyglugluaspglyvalaspasnserhismetasp
180185190
alaseralaleutyrthrglnprogluaspvalasptyralatyrthr
195200205
gluleuserlysileserproargphethrilealaalaserphegly
210215220
asnvalhisglyvaltyrlysproglyasnvalvalleuthrprothr
225230235240
ileleuargaspserglnglutyrvalserlyslyshisasnleupro
245250255
hisasnserleuasnphevalphehisglyglyserglyserthrala
260265270
glngluilelysaspservalsertyrglyvalvallysmetasnile
275280285
aspthraspthrglntrpalathrtrpgluglyvalleuasntyrtyr
290295300
lysalaasnglualatyrleuglnglyglnleuglyasnprolysgly
305310315320
gluaspglnproasnlyslystyrtyraspproargvaltrpleuarg
325330335
alaglyglnthrsermetilealaargleuglulysalapheglnglu
340345350
leuasnalaileaspvalleu
355
<210>36
<211>255
<212>prt
<213>大肠杆菌
<400>36
metarghisproleuvalmetglyasntrplysleuasnglyserarg
151015
hismetvalhisgluleuvalserasnleuarglysgluleualagly
202530
valalaglycysalavalalailealaproproglumettyrileasp
354045
metalalysargglualagluglyserhisilemetleuglyalagln
505560
asnvalaspleuasnleuserglyalaphethrglygluthrserala
65707580
alametleulysaspileglyalaglntyrileileileglyhisser
859095
gluargargthrtyrhislysgluseraspgluleuilealalyslys
100105110
phealavalleulysgluglnglyleuthrprovalleucysilegly
115120125
gluthrglualagluasnglualaglylysthrglugluvalcysala
130135140
argglnileaspalavalleulysthrglnglyalaalaalapheglu
145150155160
glyalavalilealatyrgluprovaltrpalaileglythrglylys
165170175
seralathrproalaglnalaglnalavalhislyspheileargasp
180185190
hisilealalysvalaspalaasnilealagluglnvalileilegln
195200205
tyrglyglyservalasnalaserasnalaalagluleuphealagln
210215220
proaspileaspglyalaleuvalglyglyalaserleulysalaasp
225230235240
alaphealavalilevallysalaalaglualaalalysglnala
245250255
<210>37
<211>335
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>37
metalavallysvalglyileasnglypheglyargileglyargasn
151015
valpheargalaalaleulysasnproaspilegluvalvalalaval
202530
asnaspleuthraspalaasnthrleualahisleuleulystyrasp
354045
servalhisglyargleuaspalagluvalservalasnglyasnasn
505560
leuvalvalasnglylysgluileilevallysalagluargasppro
65707580
gluasnleualatrpglygluileglyvalaspilevalvalgluser
859095
thrglyargphethrlysarggluaspalaalalyshisleugluala
100105110
glyalalyslysvalileileseralaproalalysasngluaspile
115120125
thrilevalmetglyvalasnglnasplystyraspprolysalahis
130135140
hisvalileserasnalasercysthrthrasncysleualaprophe
145150155160
alalysvalleuhisgluglnpheglyilevalargglymetmetthr
165170175
thrvalhissertyrthrasnaspglnargileleuaspleuprohis
180185190
lysaspleuargargalaargalaalaalagluserileileprothr
195200205
thrthrglyalaalalysalavalalaleuvalleuprogluleulys
210215220
glylysleuasnglymetalametargvalprothrproasnvalser
225230235240
valvalaspleuvalalagluleuglulysgluvalthrvalgluglu
245250255
valasnalaalaleulysalaalaalagluglygluleulysglyile
260265270
leualatyrserglugluproleuvalserargasptyrasnglyser
275280285
thrvalserserthrileaspalaleuserthrmetvalileaspgly
290295300
lysmetvallysvalvalsertrptyraspasngluthrglytyrser
305310315320
hisargvalvalaspleualaalatyrilealaserlysglyleu
325330335
<210>38
<211>335
<212>prt
<213>人工序列
<220>
<223>mgap突变p191d
<400>38
metalavallysvalglyileasnglypheglyargileglyargasn
151015
valpheargalaalaleulysasnproaspilegluvalvalalaval
202530
asnaspleuthraspalaasnthrleualahisleuleulystyrasp
354045
servalhisglyargleuaspalagluvalservalasnglyasnasn
505560
leuvalvalasnglylysgluileilevallysalagluargasppro
65707580
gluasnleualatrpglygluileglyvalaspilevalvalgluser
859095
thrglyargphethrlysarggluaspalaalalyshisleugluala
100105110
glyalalyslysvalileileseralaproalalysasngluaspile
115120125
thrilevalmetglyvalasnglnasplystyraspprolysalahis
130135140
hisvalileserasnalasercysthrthrasncysleualaprophe
145150155160
alalysvalleuhisgluglnpheglyilevalargglymetmetthr
165170175
thrvalhissertyrthrasnaspglnargileleuaspleuasphis
180185190
lysaspleuargargalaargalaalaalagluserileileprothr
195200205
thrthrglyalaalalysalavalalaleuvalleuprogluleulys
210215220
glylysleuasnglymetalametargvalprothrproasnvalser
225230235240
valvalaspleuvalalagluleuglulysgluvalthrvalgluglu
245250255
valasnalaalaleulysalaalaalagluglygluleulysglyile
260265270
leualatyrserglugluproleuvalserargasptyrasnglyser
275280285
thrvalserserthrileaspalaleuserthrmetvalileaspgly
290295300
lysmetvallysvalvalsertrptyraspasngluthrglytyrser
305310315320
hisargvalvalaspleualaalatyrilealaserlysglyleu
325330335
<210>39
<211>335
<212>prt
<213>人工序列
<220>
<223>mgap突变d34a/l35r/t36k
<400>39
metalavallysvalglyileasnglypheglyargileglyargasn
151015
valpheargalaalaleulysasnproaspilegluvalvalalaval
202530
asnalaarglysaspalaasnthrleualahisleuleulystyrasp
354045
servalhisglyargleuaspalagluvalservalasnglyasnasn
505560
leuvalvalasnglylysgluileilevallysalagluargasppro
65707580
gluasnleualatrpglygluileglyvalaspilevalvalgluser
859095
thrglyargphethrlysarggluaspalaalalyshisleugluala
100105110
glyalalyslysvalileileseralaproalalysasngluaspile
115120125
thrilevalmetglyvalasnglnasplystyraspprolysalahis
130135140
hisvalileserasnalasercysthrthrasncysleualaprophe
145150155160
alalysvalleuhisgluglnpheglyilevalargglymetmetthr
165170175
thrvalhissertyrthrasnaspglnargileleuaspleuprohis
180185190
lysaspleuargargalaargalaalaalagluserileileprothr
195200205
thrthrglyalaalalysalavalalaleuvalleuprogluleulys
210215220
glylysleuasnglymetalametargvalprothrproasnvalser
225230235240
valvalaspleuvalalagluleuglulysgluvalthrvalgluglu
245250255
valasnalaalaleulysalaalaalagluglygluleulysglyile
260265270
leualatyrserglugluproleuvalserargasptyrasnglyser
275280285
thrvalserserthrileaspalaleuserthrmetvalileaspgly
290295300
lysmetvallysvalvalsertrptyraspasngluthrglytyrser
305310315320
hisargvalvalaspleualaalatyrilealaserlysglyleu
325330335
<210>40
<211>394
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>40
metasnlyslysthrileargaspvalaspvalargglylysargval
151015
phecysargvalasppheasnvalprometgluglnglyalailethr
202530
aspaspthrargileargalaalaleuprothrileargtyrleuile
354045
gluhisglyalalysvalileleualaserhisleuglyargprolys
505560
glylysvalvalglugluleuargleuaspalavalalalysargleu
65707580
glygluleuleugluargprovalalalysthrasnglualavalgly
859095
aspgluvallysalaalavalaspargleuasngluglyaspvalleu
100105110
leuleugluasnvalargphetyrproglygluglulysasnasppro
115120125
gluleualalysalaphealagluleualaaspleutyrvalasnasp
130135140
alapheglyalaalahisargalahisalaserthrgluglyileala
145150155160
histyrleuproalavalalaglypheleumetglulysgluleuglu
165170175
valleuglylysalaleuserasnproaspargprophethralaile
180185190
ileglyglyalalysvallysasplysileglyvalileaspasnleu
195200205
leuglulysvalaspasnleuileileglyglyglyleualatyrthr
210215220
phevallysalaleuglyhisaspvalglylysserleuleugluglu
225230235240
asplysilegluleualalysserphemetglulysalalysglulys
245250255
glyvalargphetyrmetprovalaspvalvalvalalaaspargphe
260265270
alaasnaspalaasnthrlysvalvalproileaspalaileproala
275280285
asptrpseralaleuaspileglyprolysthrarggluleutyrarg
290295300
aspvalilearggluserlysleuvalvaltrpasnglyprometgly
305310315320
valpheglumetaspalaphealahisglythrlysalailealaglu
325330335
alaleualaglualaleuaspthrtyrservalileglyglyglyasp
340345350
seralaalaalavalglulyspheglyleualaasplysmetasphis
355360365
ileserthrglyglyglyalaserleugluphemetgluglylysgln
370375380
leuproglyvalvalalaleugluasplys
385390
<210>41
<211>470
<212>prt
<213>嗜热脱氮土芽孢杆菌
<400>41
metalalysglnglnileglyvalileglyleualavalmetglylys
151015
asnleualaleuasnilegluserargglytyrservalalavaltyr
202530
asnargserargglulysthraspglupheleugluglualalysgly
354045
lysasnilevalglythrtyrserileglugluphevalasnalaleu
505560
glulysproarglysileleuleumetvallysalaglyalaprothr
65707580
aspalathrilegluglnleulysprotyrleuglulysglyaspile
859095
leuileaspglyglyasnthrtyrphelysaspthrglnargargasn
100105110
glugluleualalysleuglyilehispheileglythrglyvalser
115120125
glyglyglugluglyalaleulysglyproserilemetproglygly
130135140
glnlysglualahisgluleuvalargproilepheglualaileala
145150155160
alalysvalaspglygluprocysthrthrtyrileglyproaspgly
165170175
alaglyhistyrvallysmetvalhisasnglyileglutyrglyasp
180185190
metglnleuilealaglualatyrpheleuleulyshisvalleugly
195200205
metaspalaalagluleuhisgluvalphealaasptrpasnlysgly
210215220
gluleuasnsertyrleuilegluilethralaaspilephethrlys
225230235240
ileaspaspgluthrglylysproleuvalaspvalileleuasplys
245250255
alaglyglnlysglythrglylystrpthrserglnasnalaleuasp
260265270
leuglyvalproleuproileilethrgluservalphealaargphe
275280285
ileseralametlysaspgluargvallysalaserlysleuleuser
290295300
glyproalavallysprophegluglyaspargasphispheileglu
305310315320
alavalargargalaleutyrmetserlysilecyssertyralagln
325330335
glyphealaglnmetlysalaalaseraspglutyrasntrpasnleu
340345350
argtyrglyaspilealametilepheargglyglycysileilearg
355360365
alaglnpheleuglnlysilelysglualatyraspargaspproala
370375380
leuproasnleuleuleuaspprotyrphelysasnilevalgluser
385390395400
tyrglnaspserleuarggluilevalalathralaalametarggly
405410415
ileprovalproalaphealaseralaleualatyrtyraspsertyr
420425430
argasngluvalleuproalaasnleuileglnalaglnargasptyr
435440445
pheglyalahisthrtyrgluargvalasplysgluglyilephehis
450455460
thrglutrpleualalys
465470
<210>42
<211>437
<212>prt
<213>大肠杆菌
<400>42
metserlysilevallysileileglyarggluileileaspserarg
151015
glyasnprothrvalglualagluvalhisleugluglyglypheval
202530
glymetalaalaalaproserglyalaserthrglyserarggluala
354045
leugluleuargaspglyasplysserargpheleuglylysglyval
505560
thrlysalavalalaalavalasnglyproilealaglnalaleuile
65707580
glylysaspalalysaspglnalaglyileasplysilemetileasp
859095
leuaspglythrglulyslysserlyspheglyalaasnalaileleu
100105110
alavalserleualaasnalalysalaalaalaalaalalysglymet
115120125
proleutyrgluhisilealagluleuasnglythrproglylystyr
130135140
sermetprovalprometmetasnileileasnglyglygluhisala
145150155160
aspasnasnvalaspileglngluphemetileglnprovalglyala
165170175
lysthrvallysglualaileargmetglysergluvalphehishis
180185190
leualalysvalleulysalalysglymetasnthralavalglyasp
195200205
gluglyglytyralaproasnleuglyserasnaspglualaleuala
210215220
valilealaglualavallysalaalaglytyrgluleuglylysasp
225230235240
ilethrleualametaspcysalaalasergluphetyrlysaspgly
245250255
lystyrvalleualaglygluglyasnlysalaphethrsergluglu
260265270
phethrhispheleuglugluleuthrlysglntyrproilevalser
275280285
ilegluaspglyleuaspgluserasptrpaspglyphealatyrgln
290295300
thrlysvalleuglyasplysileglnleuvalglyaspaspleuphe
305310315320
valthrasnthrlysileleulysgluglyileglulysglyileala
325330335
asnsertyrleuilelyspheasnglnileglyserleuthrgluthr
340345350
leualaalailelysmetalalysaspalaglytyrthralavalile
355360365
serhisargserglygluthrgluaspalathrilealaaspleuala
370375380
valglythralaalaglyglnilelysthrglysermetserargser
385390395400
aspargvalalalystyrasnglnleuileargilegluglualaleu
405410415
glyglulysalaargthrthrvalvallysargserlysalaarghis
420425430
lysthrasppheile
435
<210>43
<211>587
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>43
metlysarglysthrlysilevalcysthrileglyproalaserglu
151015
servalasplysleuvalglnleumetglualaglymetasnvalala
202530
argleuasnpheserhisglyasphisglugluhisglyargargile
354045
alaasnileargglualaalalysargthrglyargthrvalalaile
505560
leuleuaspthrlysglyprogluileargthrhisasnmetgluasn
65707580
glyalailegluleulysgluglyserlysleuvalilesermetser
859095
gluvalleuglythrproglulysileservalthrtyrproserleu
100105110
ileaspaspvalservalglyalalysileleuleuaspaspglyleu
115120125
ileserleugluvalasnalavalasplysglnalaglygluileval
130135140
thrthrvalleuasnglyglyvalleulysasnlyslysglyvalasn
145150155160
valproglyvallysvalasnleuproglyilethrglulysasparg
165170175
alaaspileleupheglyileargglnglyileasppheilealaala
180185190
serphevalargargalaseraspvalleugluilearggluleuleu
195200205
glualahisaspalaleuhisileglnileilealalysilegluasn
210215220
glugluglyvalalaasnileaspgluileleuglualaalaaspgly
225230235240
leumetvalalaargglyaspleuglyvalgluileproalagluglu
245250255
valproleuileglnlysleuleuilelyslyscysasnmetleugly
260265270
lysprovalilethralathrglnmetleuaspsermetglnargasn
275280285
proargprothrargalaglualaseraspvalalaasnalailephe
290295300
aspglythraspalavalmetleuserglygluthralaalaglygln
305310315320
tyrprovalglualavallysthrmethisglnilealaleuargthr
325330335
gluglnalaleugluhisargaspileleuserglnargthrlysglu
340345350
serglnthrthrilethraspalaileglyglnservalalahisthr
355360365
alaleuasnleuaspvalalaalailevalthrprothrvalsergly
370375380
lysthrproglnmetvalalalystyrargprolysalaproileile
385390395400
alavalthrserasnglualavalserargargleualaleuvaltrp
405410415
glyvaltyrthrlysglualaprohisvalasnthrthraspglumet
420425430
leuaspvalalavalaspalaalavalargserglyleuvallyshis
435440445
glyaspleuvalvalilethralaglyvalprovalglygluthrgly
450455460
serthrasnleumetlysvalhisvalileseraspleuleualalys
465470475480
glyglnglyileglyarglysseralapheglylysalavalvalala
485490495
lysthralagluglualaargglnlysmetvalaspglyglyileleu
500505510
valthrvalserthraspalaaspmetmetproalaileglulysala
515520525
alaalaileilethrglugluglyglyleuthrserhisalaalaval
530535540
valglyleuserleuglyileprovalilevalglyvalgluasnala
545550555560
thrthrleuphelysaspglyglngluilethrvalaspglyglyphe
565570575
glyalavaltyrargglyhisalaservalleu
580585
<210>44
<211>475
<212>prt
<213>运动发酵单胞菌
<400>44
metthrgluglyleupheproargglyarglysvalargvalvalser
151015
thrleuglyproalaserserthralagluglnileargaspargphe
202530
leualaglyalaaspvalpheargileasnmetserhisglythrhis
354045
aspglulyslysvalilevalaspasnileargalaleuglulysglu
505560
pheasnargprothrthrileleupheaspleuglnglyprolysleu
65707580
argvalglyaspphelysgluglylysvalglnleulysgluglygln
859095
thrphethrpheaspglnaspprothrleuglyaspgluthrargval
100105110
asnleuprohisprogluilephelysalaleuasplysglyhisarg
115120125
leuleuleuaspaspglylysilevalvalargcysvalgluserser
130135140
prothrlysilevalthrargvalgluvalproglyproleuserasp
145150155160
hislysglypheasnvalproaspvalvalileproleualaalaleu
165170175
thrprolysasparglysaspleuaspphealaleulysglulysala
180185190
asptrpvalalaleuserphevalglnargvalgluaspvalileglu
195200205
alalysgluleuilelysglyargalaproleuleuvallysleuglu
210215220
lysproalaalailegluasnleugluserileleualaalathrasp
225230235240
alavalmetvalalaargglyaspleuglyvalglucysleuproglu
245250255
servalproprothrglnlysargilevalgluargserargglnleu
260265270
glylysprovalvalvalalathralametleuglusermetilelys
275280285
alaproalaprothrargalagluvalseraspvalalaasnalaile
290295300
tyrgluglyalaaspglyilemetleuseralagluseralaalagly
305310315320
asptrpprohisglualavalasnmetmethisargilealasertyr
325330335
valgluasnalaproglytyrilegluargvalargphethrprothr
340345350
proalagluprothrthrvalaspalaleualagluasnalaserlys
355360365
thralagluthrvalglyalalysalaileilevalphethrgluthr
370375380
glylysthralaglnargvalserargalaargprovalalaproile
385390395400
leuserleuthrproaspalagluvalalaargargleuglyleuval
405410415
trpglyalaglnprovalglnvalserthrvallysthrleuaspglu
420425430
alalyslysleualaalagluthralalyslystyrglyphealalys
435440445
alaglyasplysleuvalvalvalalaglyglupropheglylysala
450455460
glythrthrasnilevalaspvalilegluala
465470475
<210>45
<211>531
<212>prt
<213>穴兔
<400>45
metserlysserhisserglualaglyseralapheileglnthrgln
151015
glnleuhisalaalametalaaspthrpheleugluhismetcysarg
202530
leuaspileaspseralaproilethralaargasnthrglyileile
354045
cysthrileglyproalaserargservalgluthrleulysglumet
505560
ilelysserglymetasnvalalaargmetasnpheserhisglythr
65707580
hisglutyrhisalagluthrilelysasnvalargthralathrglu
859095
serphealaseraspproileleutyrargprovalalavalalaleu
100105110
aspthrlysglyprogluileargthrglyleuilelysglysergly
115120125
thralagluvalgluleulyslysglyalathrleulysilethrleu
130135140
aspasnalatyrmetglulyscysaspgluasnileleutrpleuasp
145150155160
tyrlysasnilecyslysvalvalaspvalglyserlysvaltyrval
165170175
aspaspglyleuileserleuglnvallysglnlysglyproaspphe
180185190
leuvalthrgluvalgluasnglyglypheleuglyserlyslysgly
195200205
valasnleuproglyalaalavalaspleuproalavalserglulys
210215220
aspileglnaspleulyspheglyvalgluglnaspvalaspmetval
225230235240
phealaserpheilearglysalaalaaspvalhisgluvalarglys
245250255
ileleuglyglulysglylysasnilelysileileserlysileglu
260265270
asnhisgluglyvalargargpheaspgluileleuglualaserasp
275280285
glyilemetvalalaargglyaspleuglyilegluileproalaglu
290295300
lysvalpheleualaglnlysmetileileglyargcysasnargala
305310315320
glylysprovalilecysalathrglnmetleuglusermetilelys
325330335
lysproargprothrargalagluglyseraspvalalaasnalaval
340345350
leuaspglyalaaspcysilemetleuserglygluthralalysgly
355360365
asptyrproleuglualavalargmetglnhisleuilealaargglu
370375380
alaglualaalametphehisarglysleupheglugluleualaarg
385390395400
alaserserhisserthraspleumetglualametalametglyser
405410415
valglualasertyrlyscysleualaalaalaleuilevalleuthr
420425430
gluserglyargseralahisglnvalalaargtyrargproargala
435440445
proileilealavalthrargasnhisglnthralaargglnalahis
450455460
leutyrargglyilepheprovalvalcyslysaspprovalglnglu
465470475480
alatrpalagluaspvalaspleuargvalasnleualametasnval
485490495
glylysalaargglyphephelyslysglyaspvalvalilevalleu
500505510
thrglytrpargproglyserglyphethrasnthrmetargvalval
515520525
provalpro
530
<210>46
<211>592
<212>prt
<213>绿色气球菌
<400>46
metseraspasnlysileasnileglyleualavalmetlysileleu
151015
glusertrpglyalaaspthriletyrglyileproserglythrleu
202530
serserleumetaspalametglygluglugluasnasnvallysphe
354045
leuglnvallyshisglugluvalglyalametalaalavalmetgln
505560
serlyspheglyglyasnleuglyvalthrvalglyserglyglypro
65707580
glyalaserhisleuileasnglyleutyraspalaalametaspasn
859095
ileprovalvalalaileleuglyserargproglnarggluleuasn
100105110
metaspalapheglngluleuasnglnasnpromettyrasphisile
115120125
alavaltyrasnargargvalalatyralagluglnleuprolysleu
130135140
valaspglualaalaargmetalailealalysargglyvalalaval
145150155160
leugluvalproglyaspphealalysvalgluileaspasnaspgln
165170175
trptyrserseralaasnserleuarglystyrgluproilealapro
180185190
alaalaglnaspileaspalaalavalgluleuleuasnasnserlys
195200205
argprovaliletyralaglyileglythrmetglyhisglyproala
210215220
valglngluleualaarglysilelysalaprovalilethrthrgly
225230235240
lysasnphegluthrpheglutrpasppheglualaleuthrglyser
245250255
thrtyrargvalglytrplysproalaasngluthrileleugluala
260265270
aspthrvalleuphealaglyserasnpheprophesergluvalglu
275280285
glythrpheargasnvalaspasnpheileglnileaspileasppro
290295300
alametleuglylysarghishisalaaspvalalaileleuglyasp
305310315320
alaglyleualaileaspgluileleuasnlysvalaspalavalglu
325330335
gluseralatrptrpthralaasnleulysasnilealaasntrparg
340345350
glutyrileasnmetleugluthrlysglugluglyaspleuglnphe
355360365
tyrglnvaltyrasnalaileasnasnhisalaaspgluaspalaile
370375380
tyrserileaspvalglyasnserthrglnthrserilearghisleu
385390395400
hismetthrprolysasnmettrpargthrserproleuphealathr
405410415
metglyilealaileproglyglyleuglyalalysasnthrtyrpro
420425430
aspargglnvaltrpasnileileglyaspglyalaphesermetthr
435440445
tyrproaspvalvalthrasnvalargtyrasnmetprovalileasn
450455460
valvalpheserasnthrglutyralapheilelysasnlystyrglu
465470475480
aspthrasnlysasnleupheglyvalaspphethraspvalasptyr
485490495
alalysilealaglualaglnglyalalysglyphethrvalserarg
500505510
ilegluaspmetaspargvalmetalaglualavalalaalaasnlys
515520525
alaglyhisthrvalvalileaspcyslysilethrglnaspargpro
530535540
ileprovalgluthrleulysleuaspserlysleutyrsergluasp
545550555560
gluilelysalatyrlysgluargtyrglualaalaasnleuvalpro
565570575
pheargglutyrleuglualagluglyleugluserlystyrilelys
580585590
<210>47
<211>393
<212>prt
<213>钩虫贪铜菌h16
<400>47
metthraspvalvalilevalseralaalaargthralavalglylys
151015
pheglyglyserleualalysileproalaprogluleuglyalaval
202530
valilelysalaalaleugluargalaglyvallysprogluglnval
354045
sergluvalilemetglyglnvalleuthralaglyserglyglnasn
505560
proalaargglnalaalailelysalaglyleuproalametvalpro
65707580
alametthrileasnlysvalcysglyserglyleulysalavalmet
859095
leualaalaasnalailemetalaglyaspalagluilevalvalala
100105110
glyglyglngluasnmetseralaalaprohisvalleuproglyser
115120125
argaspglypheargmetglyaspalalysleuvalaspthrmetile
130135140
valaspglyleutrpaspvaltyrasnglntyrhismetglyilethr
145150155160
alagluasnvalalalysglutyrglyilethrargglualaglnasp
165170175
gluphealavalglyserglnasnlysalaglualaalaglnlysala
180185190
glylyspheaspglugluilevalprovalleuileproglnarglys
195200205
glyaspprovalalaphelysthraspgluphevalargglnglyala
210215220
thrleuaspsermetserglyleulysproalapheasplysalagly
225230235240
thrvalthralaalaasnalaserglyleuasnaspglyalaalaala
245250255
valvalvalmetseralaalalysalalysgluleuglyleuthrpro
260265270
leualathrilelyssertyralaasnalaglyvalaspprolysval
275280285
metglymetglyprovalproalaserlysargalaleuserargala
290295300
glutrpthrproglnaspleuaspleumetgluileasnglualaphe
305310315320
alaalaglnalaleualavalhisglnglnmetglytrpaspthrser
325330335
lysvalasnvalasnglyglyalailealaileglyhisproilegly
340345350
alaserglycysargileleuvalthrleuleuhisglumetlysarg
355360365
argaspalalyslysglyleualaserleucysileglyglyglymet
370375380
glyvalalaleualavalgluarglys
385390
<210>48
<211>383
<212>prt
<213>粪肠球菌
<400>48
metthrileglyileasplysileserphephevalproprotyrtyr
151015
ileaspmetthralaleualaglualaargasnvalaspproglylys
202530
phehisileglyileglyglnaspglnmetalavalasnproileser
354045
glnaspilevalthrphealaalaasnalaalaglualaileleuthr
505560
lysgluasplysglualaileaspmetvalilevalglythrgluser
65707580
serileaspgluserlysalaalaalavalvalleuhisargleumet
859095
glyileglnprophealaargserphegluilelysglualacystyr
100105110
glyalathralaglyleuglnleualalysasnhisvalalaleuhis
115120125
proasplyslysvalleuvalvalalaalaaspilealalystyrgly
130135140
leuasnserglyglygluprothrglnglyalaglyalavalalamet
145150155160
leuvalalasergluproargileleualaleulysgluaspasnval
165170175
metleuthrglnaspiletyraspphetrpargprothrglyhispro
180185190
tyrprometvalaspglyproleuserasngluthrtyrileglnser
195200205
phealaglnvaltrpaspgluhislyslysargthrglyleuaspphe
210215220
alaasptyraspalaleualaphehisileprotyrthrlysmetgly
225230235240
lyslysalaleuleualalysileseraspglnthrglualaglugln
245250255
gluargileleualaargtyrglugluserileiletyrserargarg
260265270
valglyasnleutyrthrserserleutyrleuglyleuileserleu
275280285
leugluasnalathrthrleuthralaglyasnglnileglyleuphe
290295300
sertyrglyserglyalavalalagluphephethrglygluleuval
305310315320
alaglytyrglnasnhisleuglnlysgluthrhisleualaleuleu
325330335
aspasnargthrgluleuserilealaglutyrglualametpheala
340345350
gluthrleuaspthraspileaspglnthrleugluaspgluleulys
355360365
tyrserileseralaileasnasnthrvalargsertyrargasn
370375380
<210>49
<211>803
<212>prt
<213>粪肠球菌
<400>49
metlysthrvalvalileileaspalaleuargthrproileglylys
151015
tyrlysglyserleuserglnvalseralavalaspleuglythrhis
202530
valthrthrglnleuleulysarghisserthrileserglugluile
354045
aspglnvalilepheglyasnvalleuglnalaglyasnglyglnasn
505560
proalaargglnilealaileasnserglyleuserhisgluilepro
65707580
alametthrvalasngluvalcysglyserglymetlysalavalile
859095
leualalysglnleuileglnleuglyglualagluvalleuileala
100105110
glyglyilegluasnmetserglnalaprolysleuglnargpheasn
115120125
tyrgluthrglusertyraspalaprophesersermetmettyrasp
130135140
glyleuthraspalapheserglyglnalametglyleuthralaglu
145150155160
asnvalalaglulystyrhisvalthrargglugluglnaspglnphe
165170175
servalhisserglnleulysalaalaglnalaglnalagluglyile
180185190
phealaaspgluilealaproleugluvalserglythrleuvalglu
195200205
lysaspgluglyileargproasnserservalglulysleuglythr
210215220
leulysthrvalphelysgluaspglythrvalthralaglyasnala
225230235240
serthrileasnaspglyalaseralaleuileilealaserglnglu
245250255
tyralaglualahisglyleuprotyrleualaileileargaspser
260265270
valgluvalglyileaspproalatyrmetglyileserproilelys
275280285
alaileglnlysleuleualaargasnglnleuthrthrglugluile
290295300
aspleutyrgluileasnglualaphealaalathrserilevalval
305310315320
glnarggluleualaleuprogluglulysvalasniletyrglygly
325330335
glyileserleuglyhisalaileglyalathrglyalaargleuleu
340345350
thrserleusertyrglnleuasnglnlysglulyslystyrglyval
355360365
alaserleucysileglyglyglyleuglyleualametleuleuglu
370375380
argproglnglnlyslysasnserargphetyrglnmetserproglu
385390395400
gluargleualaserleuleuasngluglyglnileseralaaspthr
405410415
lyslysgluphegluasnthralaleuserserglnilealaasnhis
420425430
metilegluasnglnilesergluthrgluvalprometglyvalgly
435440445
leuhisleuthrvalaspgluthrasptyrleuvalprometalathr
450455460
glugluproservalilealaalaleuserasnglyalalysileala
465470475480
glnglyphelysthrvalasnglnglnargleumetargglyglnile
485490495
valphetyraspvalalaaspalagluserleuileaspgluleugln
500505510
valarggluthrgluilepheglnglnalagluleusertyrproser
515520525
ilevallysargglyglyglyleuargaspleuglntyrargalaphe
530535540
aspgluserphevalservalasppheleuvalaspvallysaspala
545550555560
metglyalaasnilevalasnalametleugluglyvalalagluleu
565570575
pheargglutrpphealagluglnlysileleupheserileleuser
580585590
asntyralathrgluservalvalthrmetlysthralaileproval
595600605
serargleuserlysglyserasnglyarggluilealaglulysile
610615620
valleualaserargtyralaserleuaspprotyrargalavalthr
625630635640
hisasnlysglyilemetasnglyileglualavalvalleualathr
645650655
glyasnaspthrargalavalseralasercyshisalaphealaval
660665670
lysgluglyargtyrglnglyleuthrsertrpthrleuaspglyglu
675680685
glnleuileglygluileservalproleualaleualathrvalgly
690695700
glyalathrlysvalleuprolysserglnalaalaalaaspleuleu
705710715720
alavalthraspalalysgluleuserargvalvalalaalavalgly
725730735
leualaglnasnleualaalaleuargalaleuvalsergluglyile
740745750
glnlysglyhismetalaleuglnalaargserleualametthrval
755760765
glyalathrglylysgluvalglualavalalaglnglnleulysarg
770775780
glnlysthrmetasnglnaspargalaleualaileleuasnaspleu
785790795800
arglysgln
<210>50
<211>301
<212>prt
<213>马氏甲烷八叠球菌go1
<400>50
metvalsercysseralaproglylysiletyrleupheglygluhis
151015
alavalvaltyrglygluthralailealacysalavalgluleuarg
202530
thrargvalargalagluleuasnaspserilethrileglnsergln
354045
ileglyargthrglyleuasppheglulyshisprotyrvalserala
505560
valileglulysmetarglysserileproileasnglyvalpheleu
65707580
thrvalaspseraspileprovalglyserglyleuglyserserala
859095
alavalthrilealaserileglyalaleuasngluleupheglyphe
100105110
glyleuserleuglngluilealalysleuglyhisgluilegluile
115120125
lysvalglnglyalaalaserprothraspthrtyrvalserthrphe
130135140
glyglyvalvalthrileprogluargarglysleulysthrproasp
145150155160
cysglyilevalileglyaspthrglyvalpheserserthrlysglu
165170175
leuvalalaasnvalargglnleuargglusertyrproaspleuile
180185190
gluproleumetthrserileglylysileserargileglyglugln
195200205
leuvalleuserglyasptyralaserileglyargleumetasnval
210215220
asnglnglyleuleuaspalaleuglyvalasnileleugluleuser
225230235240
glnleuiletyrseralaargalaalaglyalapheglyalalysile
245250255
thrglyalaglyglyglyglycysmetvalalaleuthralaproglu
260265270
lyscysasnglnvalalaglualavalalaglyalaglyglylysval
275280285
thrilethrlysprothrgluglnglyleulysvalasp
290295300
<210>51
<211>335
<212>prt
<213>肺炎链球菌
<400>51
metilealavallysthrcysglylysleutyrtrpalaglyglutyr
151015
alaileleugluproglyglnleualaleuilelysaspileproile
202530
tyrmetargalagluilealapheseraspsertyrargiletyrser
354045
aspmetpheaspphealavalaspleuargproasnproasptyrser
505560
leuileglngluthrilealaleumetglyasppheleualavalarg
65707580
glyglnasnleuargpropheserleualailetyrglylysmetglu
859095
arggluglylyslyspheglyleuglyserserglyservalvalval
100105110
leuvalvallysalaleuleualaleutyrasnleuservalaspgln
115120125
asnleuleuphelysleuthrseralavalleuleulysargglyasp
130135140
asnglysermetglyaspleualacysilealaalagluaspleuval
145150155160
leutyrglnserpheaspargglnlysvalalaalatrpleugluglu
165170175
gluasnleualathrvalleugluargasptrpglypheserileser
180185190
glnvallysprothrleuglucysasppheleuvalglytrpthrlys
195200205
gluvalalavalserserhismetvalglnglnilelysglnasnile
210215220
asnglnasnpheleuthrserserlysgluthrvalvalserleuval
225230235240
glualaleugluglnglylysserglulysileilegluglnvalglu
245250255
valalaserlysleuleugluglyleuserthraspiletyrthrpro
260265270
leuleuargglnleulysglualaserglnaspleuglnalavalala
275280285
lysserserglyalaglyglyglyaspcysglyilealaleuserphe
290295300
aspalaglnserthrlysthrleulysasnargtrpalaaspleugly
305310315320
ilegluleuleutyrglngluargileglyhisaspasplysser
325330335
<210>52
<211>344
<212>prt
<213>肺炎链球菌
<400>52
mettyrhisserleuglyasnglnpheaspthrargthrargthrser
151015
arglysileargarggluargsercysseraspmetaspargglupro
202530
valthrvalargsertyralaasnilealaileilelystyrtrpgly
354045
lyslyslysglulysglumetvalproalathrserserileserleu
505560
thrleugluasnmettyrthrgluthrthrleuserproleuproala
65707580
asnvalthralaaspgluphetyrileasnglyglnleuglnasnglu
859095
valgluhisalalysmetserlysileileaspargtyrargproala
100105110
glygluglyphevalargileaspthrglnasnasnmetprothrala
115120125
alaglyleuserserserserserglyleuseralaleuvallysala
130135140
cysasnalatyrphelysleuglyleuaspargserglnleualagln
145150155160
glualalysphealaserglyserserserargserphetyrglypro
165170175
leuglyalatrpasplysaspserglygluiletyrprovalgluthr
180185190
aspleulysleualametilemetleuvalleugluasplyslyslys
195200205
proileserserargaspglymetlysleucysvalgluthrserthr
210215220
thrpheaspasptrpvalargglnserglulysasptyrglnaspmet
225230235240
leuiletyrleulysgluasnaspphealalysileglygluleuthr
245250255
glulysasnalaleualamethisalathrthrlysthralaserpro
260265270
alaphesertyrleuthraspalasertyrglualametasppheval
275280285
argglnleuargglulysglyglualacystyrphethrmetaspala
290295300
glyproasnvallysvalphecysglnglulysaspleugluhisleu
305310315320
sergluilepheglyglnargtyrargleuilevalserlysthrlys
325330335
aspleuserglnaspaspcyscys
340
<210>53
<211>297
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>53
metalaglnleuservalgluglnpheleuasngluglnlysglnala
151015
valgluthralaleuserargtyrilegluargleugluglyproala
202530
lysleulyslysalametalatyrserleuglualaglyglylysarg
354045
ileargproleuleuleuleuserthrvalargalaleuglylysasp
505560
proalavalglyleuprovalalacysalaileglumetilehisthr
65707580
tyrserleuilehisaspaspleuprosermetaspasnaspaspleu
859095
argargglylysprothrasnhislysvalpheglyglualametala
100105110
ileleualaglyaspglyleuleuthrtyralapheglnleuilethr
115120125
gluileaspaspgluargileproproservalargleuargleuile
130135140
gluargleualalysalaalaglyprogluglymetvalalaglygln
145150155160
alaalaaspmetgluglygluglylysthrleuthrleusergluleu
165170175
glutyrilehisarghislysthrglylysmetleuglntyrserval
180185190
hisalaglyalaleuileglyglyalaaspalaargglnthrargglu
195200205
leuaspgluphealaalahisleuglyleualapheglnileargasp
210215220
aspileleuaspilegluglyalagluglulysileglylysproval
225230235240
glyseraspglnserasnasnlysalathrtyrproalaleuleuser
245250255
leualaglyalalysglulysleualaphehisileglualaalagln
260265270
arghisleuargasnalaaspvalaspglyalaalaleualatyrile
275280285
cysgluleuvalalaalaargasphis
290295
<210>54
<211>789
<212>dna
<213>大肠杆菌
<220>
<221>cds
<222>(1)..(789)
<400>54
atgcaagtcgacctgctgggttcagcgcaatctgcgcacgcgttacac48
metglnvalaspleuleuglyseralaglnseralahisalaleuhis
151015
ctttttcaccaacattcccctcttgtgcactgcatgaccaatgatgtg96
leuphehisglnhisserproleuvalhiscysmetthrasnaspval
202530
gtgcaaacctttaccgccaataccttgctggcgctcggtgcatcgcca144
valglnthrphethralaasnthrleuleualaleuglyalaserpro
354045
gcgatggttatcgaaaccgaagaggccagtcagtttgcggctatcgcc192
alametvalilegluthrgluglualaserglnphealaalaileala
505560
agtgccttgttgattaacgttggcacactgacgcagccacgcgctcag240
seralaleuleuileasnvalglythrleuthrglnproargalagln
65707580
gcgatgcgtgctgccgttgagcaagcaaaaagctctcaaacaccctgg288
alametargalaalavalgluglnalalysserserglnthrprotrp
859095
acgcttgatccagtagcggtgggtgcgctcgattatcgccgccatttt336
thrleuaspprovalalavalglyalaleuasptyrargarghisphe
100105110
tgtcatgaacttttatcttttaaaccggcagcgatacgtggtaatgct384
cyshisgluleuleuserphelysproalaalaileargglyasnala
115120125
tcggaaatcatggcattagctggcattgctaatggcggacggggagtg432
sergluilemetalaleualaglyilealaasnglyglyargglyval
130135140
gataccactgacgccgcagctaacgcgatacccgctgcacaaacactg480
aspthrthraspalaalaalaasnalaileproalaalaglnthrleu
145150155160
gcacgggaaactggcgcaatcgtcgtggtcactggcgagatggattat528
alaarggluthrglyalailevalvalvalthrglyglumetasptyr
165170175
gttaccgatggacatcgtatcattggtattcacggtggtgatccgtta576
valthraspglyhisargileileglyilehisglyglyaspproleu
180185190
atgaccaaagtggtaggaactggctgtgcattatcggcggttgtcgct624
metthrlysvalvalglythrglycysalaleuseralavalvalala
195200205
gcctgctgtgcgttaccaggcgatacgctggaaaatgtcgcatctgcc672
alacyscysalaleuproglyaspthrleugluasnvalalaserala
210215220
tgtcactggatgaaacaagccggagaacgcgcagtcgccagaagcgag720
cyshistrpmetlysglnalaglygluargalavalalaargserglu
225230235240
gggccaggcagttttgttccacatttccttgatgcgctctggcaattg768
glyproglyserphevalprohispheleuaspalaleutrpglnleu
245250255
acgcaggaggtgcaggcatga789
thrglngluvalglnala
260
<210>55
<211>262
<212>prt
<213>大肠杆菌
<400>55
metglnvalaspleuleuglyseralaglnseralahisalaleuhis
151015
leuphehisglnhisserproleuvalhiscysmetthrasnaspval
202530
valglnthrphethralaasnthrleuleualaleuglyalaserpro
354045
alametvalilegluthrgluglualaserglnphealaalaileala
505560
seralaleuleuileasnvalglythrleuthrglnproargalagln
65707580
alametargalaalavalgluglnalalysserserglnthrprotrp
859095
thrleuaspprovalalavalglyalaleuasptyrargarghisphe
100105110
cyshisgluleuleuserphelysproalaalaileargglyasnala
115120125
sergluilemetalaleualaglyilealaasnglyglyargglyval
130135140
aspthrthraspalaalaalaasnalaileproalaalaglnthrleu
145150155160
alaarggluthrglyalailevalvalvalthrglyglumetasptyr
165170175
valthraspglyhisargileileglyilehisglyglyaspproleu
180185190
metthrlysvalvalglythrglycysalaleuseralavalvalala
195200205
alacyscysalaleuproglyaspthrleugluasnvalalaserala
210215220
cyshistrpmetlysglnalaglygluargalavalalaargserglu
225230235240
glyproglyserphevalprohispheleuaspalaleutrpglnleu
245250255
thrglngluvalglnala
260
<210>56
<211>819
<212>dna
<213>枯草芽孢杆菌
<220>
<221>cds
<222>(1)..(819)
<400>56
atggatgcacaatcagcagcaaaatgtcttacggctgtccgccggcat48
metaspalaglnseralaalalyscysleuthralavalargarghis
151015
agcccactggtgcatagcataaccaacaatgtcgtaacgaatttcaca96
serproleuvalhisserilethrasnasnvalvalthrasnphethr
202530
gcaaacggcctgctcgcgctcggcgcatcgcccgttatggcgtacgca144
alaasnglyleuleualaleuglyalaserprovalmetalatyrala
354045
aaagaagaggtcgccgatatggcgaaaattgcgggtgcactcgtttta192
lysglugluvalalaaspmetalalysilealaglyalaleuvalleu
505560
aatatcggaacactgagcaaggagtcagtcgaagcgatgatcatcgcg240
asnileglythrleuserlysgluservalglualametileileala
65707580
ggaaaatcagctaatgaacatggcgttcccgtcattcttgatcctgtc288
glylysseralaasngluhisglyvalprovalileleuaspproval
859095
ggtgccggagcaacaccgttccgcactgaatcggcacgtgacatcatt336
glyalaglyalathrpropheargthrgluseralaargaspileile
100105110
cgtgaggtgcgccttgctgcaatcagaggaaatgcggcggaaattgcc384
arggluvalargleualaalaileargglyasnalaalagluileala
115120125
cataccgtcggcgtgaccgattggctgatcaaaggtgttgatgcgggt432
histhrvalglyvalthrasptrpleuilelysglyvalaspalagly
130135140
gaaggtggaggcgacatcatccggctggctcagcaggcggcacaaaag480
gluglyglyglyaspileileargleualaglnglnalaalaglnlys
145150155160
ctaaacacggtcattgcgataactggtgaagttgatgtcatagccgac528
leuasnthrvalilealailethrglygluvalaspvalilealaasp
165170175
acgtcacatgtatacacccttcataacggccacaagctgctgacaaaa576
thrserhisvaltyrthrleuhisasnglyhislysleuleuthrlys
180185190
gtgacaggcgccggttgcctgctgacttccgtcgtcggtgcgttttgc624
valthrglyalaglycysleuleuthrservalvalglyalaphecys
195200205
gctgtggaagaaaatccattgtttgctgctattgcggccatttcttcg672
alavalglugluasnproleuphealaalailealaalaileserser
210215220
tatggggtcgccgctcagcttgccgcacagcagacggctgacaaaggc720
tyrglyvalalaalaglnleualaalaglnglnthralaasplysgly
225230235240
cctggaagctttcagattgaattgctgaacaagctttcaactgttact768
proglyserpheglnilegluleuleuasnlysleuserthrvalthr
245250255
gaacaagacgtccaagaatgggcgactatagaaagggtgactgtctca816
gluglnaspvalglnglutrpalathrilegluargvalthrvalser
260265270
tga819
<210>57
<211>272
<212>prt
<213>枯草芽孢杆菌
<400>57
metaspalaglnseralaalalyscysleuthralavalargarghis
151015
serproleuvalhisserilethrasnasnvalvalthrasnphethr
202530
alaasnglyleuleualaleuglyalaserprovalmetalatyrala
354045
lysglugluvalalaaspmetalalysilealaglyalaleuvalleu
505560
asnileglythrleuserlysgluservalglualametileileala
65707580
glylysseralaasngluhisglyvalprovalileleuaspproval
859095
glyalaglyalathrpropheargthrgluseralaargaspileile
100105110
arggluvalargleualaalaileargglyasnalaalagluileala
115120125
histhrvalglyvalthrasptrpleuilelysglyvalaspalagly
130135140
gluglyglyglyaspileileargleualaglnglnalaalaglnlys
145150155160
leuasnthrvalilealailethrglygluvalaspvalilealaasp
165170175
thrserhisvaltyrthrleuhisasnglyhislysleuleuthrlys
180185190
valthrglyalaglycysleuleuthrservalvalglyalaphecys
195200205
alavalglugluasnproleuphealaalailealaalaileserser
210215220
tyrglyvalalaalaglnleualaalaglnglnthralaasplysgly
225230235240
proglyserpheglnilegluleuleuasnlysleuserthrvalthr
245250255
gluglnaspvalglnglutrpalathrilegluargvalthrvalser
260265270
<210>58
<211>783
<212>dna
<213>詹氏甲烷暖球菌
<220>
<221>cds
<222>(1)..(783)
<400>58
atgttgactattcttaagttgggagggagcattctgtccgataaaaac48
metleuthrileleulysleuglyglyserileleuserasplysasn
151015
gttccatatagcattaagtgggataacttagaacgtattgctatggaa96
valprotyrserilelystrpaspasnleugluargilealametglu
202530
atcaaaaacgcgttagattattacaagaaccaaaataaagaaattaag144
ilelysasnalaleuasptyrtyrlysasnglnasnlysgluilelys
354045
cttattctggtacatggcggcggggcatttgggcatccagtggccaag192
leuileleuvalhisglyglyglyalapheglyhisprovalalalys
505560
aaatacctgaagattgaagacggcaaaaaaattttcatcaacatggaa240
lystyrleulysilegluaspglylyslysilepheileasnmetglu
65707580
aaaggattctgggagattcagcgtgcgatgcgccgttttaataacatc288
lysglyphetrpgluileglnargalametargargpheasnasnile
859095
atcatcgacacgcttcagagttacgatatcccagcggtctcgattcaa336
ileileaspthrleuglnsertyraspileproalavalserilegln
100105110
ccttccagctttgttgtttttggcgacaaattgatcttcgacacctct384
proserserphevalvalpheglyasplysleuilepheaspthrser
115120125
gcgatcaaagagatgttgaaacgcaaccttgtacccgttatccatggg432
alailelysglumetleulysargasnleuvalprovalilehisgly
130135140
gatatcgtcattgacgataaaaatgggtaccgtattatcagcggtgac480
aspilevalileaspasplysasnglytyrargileileserglyasp
145150155160
gacatcgtgccatatttagccaatgaactgaaggcagatttaatcctt528
aspilevalprotyrleualaasngluleulysalaaspleuileleu
165170175
tatgcaaccgacgtggacggcgtattgattgacaacaagcccattaaa576
tyralathraspvalaspglyvalleuileaspasnlysproilelys
180185190
cgcattgataagaataatatctacaagattttgaattatctttcgggt624
argileasplysasnasniletyrlysileleuasntyrleusergly
195200205
agcaattcaattgacgtcacgggggggatgaaatacaagatcgacatg672
serasnserileaspvalthrglyglymetlystyrlysileaspmet
210215220
atccgtaaaaacaaatgccgtggtttcgtgtttaatggcaacaaggca720
ilearglysasnlyscysargglyphevalpheasnglyasnlysala
225230235240
aacaacatttataaggcgctgcttggggaagtcgagggtaccgaaatc768
asnasniletyrlysalaleuleuglygluvalgluglythrgluile
245250255
gacttttctgaataa783
asppheserglu
260
<210>59
<211>260
<212>prt
<213>詹氏甲烷暖球菌
<400>59
metleuthrileleulysleuglyglyserileleuserasplysasn
151015
valprotyrserilelystrpaspasnleugluargilealametglu
202530
ilelysasnalaleuasptyrtyrlysasnglnasnlysgluilelys
354045
leuileleuvalhisglyglyglyalapheglyhisprovalalalys
505560
lystyrleulysilegluaspglylyslysilepheileasnmetglu
65707580
lysglyphetrpgluileglnargalametargargpheasnasnile
859095
ileileaspthrleuglnsertyraspileproalavalserilegln
100105110
proserserphevalvalpheglyasplysleuilepheaspthrser
115120125
alailelysglumetleulysargasnleuvalprovalilehisgly
130135140
aspilevalileaspasplysasnglytyrargileileserglyasp
145150155160
aspilevalprotyrleualaasngluleulysalaaspleuileleu
165170175
tyralathraspvalaspglyvalleuileaspasnlysproilelys
180185190
argileasplysasnasniletyrlysileleuasntyrleusergly
195200205
serasnserileaspvalthrglyglymetlystyrlysileaspmet
210215220
ilearglysasnlyscysargglyphevalpheasnglyasnlysala
225230235240
asnasniletyrlysalaleuleuglygluvalgluglythrgluile
245250255
asppheserglu
260
<210>60
<211>744
<212>dna
<213>嗜热乙酸甲烷丝菌
<220>
<221>cds
<222>(1)..(744)
<400>60
ttaaagattttgaaattgggcggtagcattattacggataagagccgc48
leulysileleulysleuglyglyserileilethrasplysserarg
151015
ttagctactgcacgtctggatcaaatttcacgtatcgcacacgaaatc96
leualathralaargleuaspglnileserargilealahisgluile
202530
tcaggcatcgagaacctgattgttgttcacggagccggttcttttggt144
serglyilegluasnleuilevalvalhisglyalaglyserphegly
354045
cacatccatgccaaaaatttcggtcttccggaacgtttctcaggagaa192
hisilehisalalysasnpheglyleuprogluargpheserglyglu
505560
gggttactgaaaacacatctgtcggtctcggatttgaatcgtatcgtc240
glyleuleulysthrhisleuservalseraspleuasnargileval
65707580
gttgaagctcttcatgatgcaggggtggacgcgctgcccttgcacccc288
valglualaleuhisaspalaglyvalaspalaleuproleuhispro
859095
ttatcaagtgtagtccttcgtgacggacgcatccaccatatgtctacc336
leuserservalvalleuargaspglyargilehishismetserthr
100105110
gaggtcattacggaaatgcttcgtcgtgatgtagtgccggtattacat384
gluvalilethrglumetleuargargaspvalvalprovalleuhis
115120125
ggggatgttgcgatggacctgtcaaagggtgccggcattgtaagtgga432
glyaspvalalametaspleuserlysglyalaglyilevalsergly
130135140
gaccagttggtttcgtatatggcacgtactctgggagctggtatggtc480
aspglnleuvalsertyrmetalaargthrleuglyalaglymetval
145150155160
gctatggggaccgatgtcgacggggttatgatcgatggtcgtgtcctt528
alametglythraspvalaspglyvalmetileaspglyargvalleu
165170175
agttgcattacacctaatgacatgcactctttggagagtcacttatta576
sercysilethrproasnaspmethisserleugluserhisleuleu
180185190
cccgcaaaaggggtagacgtcacgggtggaatgcgcggtaaactggcg624
proalalysglyvalaspvalthrglyglymetargglylysleuala
195200205
gaattagtagagctggcaggcattggaattgattcgcgtatttttaat672
gluleuvalgluleualaglyileglyileaspserargilepheasn
210215220
gccggcgttgctggtaatgtacgccgtgctttgtctggggagtcgtta720
alaglyvalalaglyasnvalargargalaleuserglygluserleu
225230235240
ggaactttgattactggacgctaa744
glythrleuilethrglyarg
245
<210>61
<211>247
<212>prt
<213>嗜热乙酸甲烷丝菌
<400>61
leulysileleulysleuglyglyserileilethrasplysserarg
151015
leualathralaargleuaspglnileserargilealahisgluile
202530
serglyilegluasnleuilevalvalhisglyalaglyserphegly
354045
hisilehisalalysasnpheglyleuprogluargpheserglyglu
505560
glyleuleulysthrhisleuservalseraspleuasnargileval
65707580
valglualaleuhisaspalaglyvalaspalaleuproleuhispro
859095
leuserservalvalleuargaspglyargilehishismetserthr
100105110
gluvalilethrglumetleuargargaspvalvalprovalleuhis
115120125
glyaspvalalametaspleuserlysglyalaglyilevalsergly
130135140
aspglnleuvalsertyrmetalaargthrleuglyalaglymetval
145150155160
alametglythraspvalaspglyvalmetileaspglyargvalleu
165170175
sercysilethrproasnaspmethisserleugluserhisleuleu
180185190
proalalysglyvalaspvalthrglyglymetargglylysleuala
195200205
gluleuvalgluleualaglyileglyileaspserargilepheasn
210215220
alaglyvalalaglyasnvalargargalaleuserglygluserleu
225230235240
glythrleuilethrglyarg
245
<210>62
<211>543
<212>dna
<213>大肠杆菌
<220>
<221>cds
<222>(1)..(543)
<400>62
atgcaaaccgagcatgtcattttattggacgagcaaggagaaccaatt48
metglnthrgluhisvalileleuleuaspgluglnglygluproile
151015
ggaactttagaaaaatacgctgcacatacagcggacacccgcttacat96
glythrleuglulystyralaalahisthralaaspthrargleuhis
202530
cttgctttttctagttggctgtttaacgataagggtcaattattagtg144
leualaphesersertrpleupheasnasplysglyglnleuleuval
354045
acgcgccgtgcgctgagcaaaaaagcatggccgggtgtttggacgaac192
thrargargalaleuserlyslysalatrpproglyvaltrpthrasn
505560
agtgtttgcggacacccccaactgggagaatccaatgaggatgcggta240
servalcysglyhisproglnleuglygluserasngluaspalaval
65707580
attcgccgttgtcgctatgaattgggtgtggagattacgccaccgaca288
ileargargcysargtyrgluleuglyvalgluilethrproprothr
859095
ccgatctaccctgatttccgttatcgcgctacggatccttcaggtatt336
proiletyrproasppheargtyrargalathraspproserglyile
100105110
gttgaaaatgaagtatgcccagtgtttgccgcgcgcacaacttctgcg384
valgluasngluvalcysprovalphealaalaargthrthrserala
115120125
cttcaaatcaacccagacgaggtcatggattaccaatggtgtgatctt432
leuglnileasnproaspgluvalmetasptyrglntrpcysaspleu
130135140
gctgacgtactgcacgggattgacgcgacaccgtgggcttttagtccc480
alaaspvalleuhisglyileaspalathrprotrpalapheserpro
145150155160
tggatggttatgcaagcgacaaatgaagaagcacgtaagcgccttcag528
trpmetvalmetglnalathrasngluglualaarglysargleugln
165170175
gcgtttactcagtaa543
alaphethrgln
180
<210>63
<211>180
<212>prt
<213>大肠杆菌
<400>63
metglnthrgluhisvalileleuleuaspgluglnglygluproile
151015
glythrleuglulystyralaalahisthralaaspthrargleuhis
202530
leualaphesersertrpleupheasnasplysglyglnleuleuval
354045
thrargargalaleuserlyslysalatrpproglyvaltrpthrasn
505560
servalcysglyhisproglnleuglygluserasngluaspalaval
65707580
ileargargcysargtyrgluleuglyvalgluilethrproprothr
859095
proiletyrproasppheargtyrargalathraspproserglyile
100105110
valgluasngluvalcysprovalphealaalaargthrthrserala
115120125
leuglnileasnproaspgluvalmetasptyrglntrpcysaspleu
130135140
alaaspvalleuhisglyileaspalathrprotrpalapheserpro
145150155160
trpmetvalmetglnalathrasngluglualaarglysargleugln
165170175
alaphethrgln
180
<210>64
<211>894
<212>dna
<213>嗜热脂肪土芽孢杆菌
<220>
<221>cds
<222>(1)..(894)
<400>64
atggcgcagctttcagttgaacagtttctcaacgagcaaaaacaggcg48
metalaglnleuservalgluglnpheleuasngluglnlysglnala
151015
gtggaaacagcgctctcccgttatatagagcgcttagaagggccggcg96
valgluthralaleuserargtyrilegluargleugluglyproala
202530
aagctgaaaaaggcgatggcgtactcattggaggccggcggcaaacga144
lysleulyslysalametalatyrserleuglualaglyglylysarg
354045
atccgtccgttgctgcttctgtccaccgttcgggcgctcggcaaagac192
ileargproleuleuleuleuserthrvalargalaleuglylysasp
505560
ccggcggtcggattgcccgtcgcctgcgcgattgaaatgatccatacg240
proalavalglyleuprovalalacysalaileglumetilehisthr
65707580
tactttttgatccatgatgatttgccgagcatggacaacgatgatttg288
tyrpheleuilehisaspaspleuprosermetaspasnaspaspleu
859095
cggcgcggcaagccgacgaaccataaagtgttcggcgaggcgatggcc336
argargglylysprothrasnhislysvalpheglyglualametala
100105110
atcttggcgggggacgggttgttgacgtacgcgtttcaattgatcacc384
ileleualaglyaspglyleuleuthrtyralapheglnleuilethr
115120125
gaaatcgacgatgagcgcatccctccttccgtccggcttcggctcatc432
gluileaspaspgluargileproproservalargleuargleuile
130135140
gaacggctggcgaaagcggccggtccggaagggatggtcgccggtcag480
gluargleualalysalaalaglyprogluglymetvalalaglygln
145150155160
gcagccgatatggaaggagaggggaaaacgctgacgctttcggagctc528
alaalaaspmetgluglygluglylysthrleuthrleusergluleu
165170175
gaatacattcatcggcataaaaccgggaaaatgctgcaatacagcgtg576
glutyrilehisarghislysthrglylysmetleuglntyrserval
180185190
cacgccggcgccttgatcggcggcgctgatgcccggcaaacgcgggag624
hisalaglyalaleuileglyglyalaaspalaargglnthrargglu
195200205
cttgacgaattcgccgcccatctaggccttgcctttcaaattcgcgat672
leuaspgluphealaalahisleuglyleualapheglnileargasp
210215220
gatattctcgatattgaaggggcagaagaaaaaatcggcaagccggtc720
aspileleuaspilegluglyalagluglulysileglylysproval
225230235240
ggcagcgaccaaagcaacaacaaagcgacgtatccagcgttgctgtcg768
glyseraspglnserasnasnlysalathrtyrproalaleuleuser
245250255
cttgccggcgcgaaggaaaagttggcgttccatatcgaggcggcgcag816
leualaglyalalysglulysleualaphehisileglualaalagln
260265270
cgccatttacggaacgctgacgttgacggcgccgcgctcgcctatatt864
arghisleuargasnalaaspvalaspglyalaalaleualatyrile
275280285
tgcgaactggtcgccgcccgcgaccattaa894
cysgluleuvalalaalaargasphis
290295
<210>65
<211>297
<212>prt
<213>嗜热脂肪土芽孢杆菌
<400>65
metalaglnleuservalgluglnpheleuasngluglnlysglnala
151015
valgluthralaleuserargtyrilegluargleugluglyproala
202530
lysleulyslysalametalatyrserleuglualaglyglylysarg
354045
ileargproleuleuleuleuserthrvalargalaleuglylysasp
505560
proalavalglyleuprovalalacysalaileglumetilehisthr
65707580
tyrpheleuilehisaspaspleuprosermetaspasnaspaspleu
859095
argargglylysprothrasnhislysvalpheglyglualametala
100105110
ileleualaglyaspglyleuleuthrtyralapheglnleuilethr
115120125
gluileaspaspgluargileproproservalargleuargleuile
130135140
gluargleualalysalaalaglyprogluglymetvalalaglygln
145150155160
alaalaaspmetgluglygluglylysthrleuthrleusergluleu
165170175
glutyrilehisarghislysthrglylysmetleuglntyrserval
180185190
hisalaglyalaleuileglyglyalaaspalaargglnthrargglu
195200205
leuaspgluphealaalahisleuglyleualapheglnileargasp
210215220
aspileleuaspilegluglyalagluglulysileglylysproval
225230235240
glyseraspglnserasnasnlysalathrtyrproalaleuleuser
245250255
leualaglyalalysglulysleualaphehisileglualaalagln
260265270
arghisleuargasnalaaspvalaspglyalaalaleualatyrile
275280285
cysgluleuvalalaalaargasphis
290295
<210>66
<211>924
<212>dna
<213>人工序列
<220>
<223>nphbm23cdna
<400>66
atgtccgaggcggccgacgtggagcgtgtttatgctgctatggaagaagctgcgggtctg60
ctgggagtggcatgtgctcgtgataagatttatccccttctttcaaccttccaggataca120
ttggttgaaggtggcagtgtggtagtgtttagcatggctagtggacgccacagcacggaa180
ctggactttagtatttcagtacccacgtcccatggtgacccatacgcaactgtcgtcgaa240
aaggggctgttccctgcaacaggccatcctgttgacgatcttttggctgatacgcagaag300
cacctgcctgtttctatgttcgccattgatggagaagtcaccggaggtttcaaaaaaact360
tatgctttctttccaactgataatatgccaggtgtggccgagttgagtgccatccccagt420
atgccaccggcggtcgcggaaaacgccgaattattcgcgcgttatgggttagataaggtg480
cagatgacgtcaatggactacaagaagcgccaggtcaatttgtacttctctgagttaagt540
gcacagactttagaagccgagtctgtccttgcgcttgttcgtgaactgggtttgcacgtg600
ccgaacgaactgggtcttaaattttgcaagcgctccttttccgtttatccgacactgaac660
tgggaaacagggaaaattgatcgtttatgttttgcggtgatttcaaacgaccctaccttg720
gtaccaagttcggacgaaggggacattgaaaaatttcacaactacgcgacgaaggcgccg780
tacgcatacgtcggcgaaaagcgtacgctggtttacgggttgacgctgagtcccaaagag840
gaatactataaattaagcgcagcgtaccatatcaccgatgtacaacgcggactgctgaag900
gcctttgatagccttgaagactaa924
<210>67
<211>924
<212>dna
<213>人工序列
<220>
<223>nphbm31cdna
<400>67
atgtccgaggcggccgacgtggagcgtgtttatgctgctatggaagaagctgcgggtctg60
ctgggagtggcatgtgctcgtgataagatttatccccttctttcaaccttccaggataca120
ttggttgaaggtggcagtgtggtagtgtttagcatggctagtggacgccacagcacggaa180
ctggactttagtatttcagtacccacgtcccatggtgacccatacgcaactgtcgtcgaa240
aaggggctgttccctgcaacaggccatcctgttgacgatcttttggctgatacgcagaag300
cacctgcctgtttctatgttcgccattgatggagaagtcaccggaggtttcaaaaaaact360
tatgctttctttccaactgataatatgccaggtgtggccgagttgagtgccatccccagt420
atgccaccggcggtcgcggaaaacgccgaattattcgcgcgttatgggttagataaggtg480
cagatgacgtcaatggactacaagaagcgccaggtcaatttgtacttctctgagttaagt540
gcacagactttagaagccgagtctgtccttgcgcttgttcgtgaactgggtttgcacgtg600
ccgaacgaactgggtcttaaattttgcaagcgctccttttccgtttatccgacactgaac660
tgggaaacagggaaaattgatcgtttatgttttagcgtgatttcaaacgaccctaccttg720
gtaccaagttcggacgaaggggacattgaaaaatttcacaactacgcgacgaaggcgccg780
tacgcatacgtcggcgaaaagcgtacgctggtttacgggttgacgctgagtcccaaagag840
gaatactataaattaggcgcagtgtaccatatcaccgatgtacaacgcggactgctgaag900
gcctttgatagccttgaagactaa924
<210>68
<211>924
<212>dna
<213>人工序列
<220>
<223>nphbm31pross10cdna
<220>
<221>cds
<222>(1)..(924)
<400>68
atgtcggaagctgccgatgtagaacgtgtctacgccgccatcgaagaa48
metserglualaalaaspvalgluargvaltyralaalailegluglu
151015
gccgcaggtttgttgggggtcgcatgcgcacgcgataagatttggccc96
alaalaglyleuleuglyvalalacysalaargasplysiletrppro
202530
ttgctgtcaacattccaggataccttggttgagggtggaagcgtagtt144
leuleuserthrpheglnaspthrleuvalgluglyglyservalval
354045
gtttttagcatggcctcggggcgtcactcaacggagctggacttctca192
valphesermetalaserglyarghisserthrgluleuasppheser
505560
atttccgtcccgcctagtcatggcgatccgtacgcgattgtggtggaa240
ileservalproproserhisglyaspprotyralailevalvalglu
65707580
aagggcttgttcccggcaactggacatccagttgatgaccttctggcg288
lysglyleupheproalathrglyhisprovalaspaspleuleuala
859095
gacattcagaagcatcttcccgtatctatgtttgcgattgacggggaa336
aspileglnlyshisleuprovalsermetphealaileaspglyglu
100105110
gttaccggggggttcaaaaaaacttatgcgttcttcccgaccgataac384
valthrglyglyphelyslysthrtyralaphepheprothraspasn
115120125
atgcccggtgtcgcggaactggcggccatcccatcgatgcctcctgca432
metproglyvalalagluleualaalaileprosermetproproala
130135140
gtcgctgaaaatgctgaactgttcgcgcgttatggcctggacaaggta480
valalagluasnalagluleuphealaargtyrglyleuasplysval
145150155160
caaatgacctcgatggattataaaaaacgtcaagtgaacctgtatttc528
glnmetthrsermetasptyrlyslysargglnvalasnleutyrphe
165170175
tccgaactgtcggctcagacgctggaggctgaatcagtacttgcttta576
sergluleuseralaglnthrleuglualagluservalleualaleu
180185190
gtgcgtgaactgggtcttcatgtcccaaacgagctgggtctgaaattt624
valarggluleuglyleuhisvalproasngluleuglyleulysphe
195200205
tgcaaacgctccttctcagtatacccaacattaaactgggacacctcg672
cyslysargserpheservaltyrprothrleuasntrpaspthrser
210215220
aagattgaccgcctttgcttctctgtaatcagtacagatccgacactt720
lysileaspargleucyspheservalileserthraspprothrleu
225230235240
gtacctagctcagacgagggagacattgaaaaatttcacaattacgct768
valproserseraspgluglyaspileglulysphehisasntyrala
245250255
acaaaggccccctatgcatatgttggagaaaagcgtacacttgtttac816
thrlysalaprotyralatyrvalglyglulysargthrleuvaltyr
260265270
ggcttgactttatctcccaaagaggagtattataaattgggtgccgtt864
glyleuthrleuserprolysgluglutyrtyrlysleuglyalaval
275280285
taccacattactgacgtacaacgcaaacttttgaaggcgttcgacagc912
tyrhisilethraspvalglnarglysleuleulysalapheaspser
290295300
cttgaggattaa924
leugluasp
305
<210>69
<211>307
<212>prt
<213>人工序列
<220>
<223>合成的构建体
<400>69
metserglualaalaaspvalgluargvaltyralaalailegluglu
151015
alaalaglyleuleuglyvalalacysalaargasplysiletrppro
202530
leuleuserthrpheglnaspthrleuvalgluglyglyservalval
354045
valphesermetalaserglyarghisserthrgluleuasppheser
505560
ileservalproproserhisglyaspprotyralailevalvalglu
65707580
lysglyleupheproalathrglyhisprovalaspaspleuleuala
859095
aspileglnlyshisleuprovalsermetphealaileaspglyglu
100105110
valthrglyglyphelyslysthrtyralaphepheprothraspasn
115120125
metproglyvalalagluleualaalaileprosermetproproala
130135140
valalagluasnalagluleuphealaargtyrglyleuasplysval
145150155160
glnmetthrsermetasptyrlyslysargglnvalasnleutyrphe
165170175
sergluleuseralaglnthrleuglualagluservalleualaleu
180185190
valarggluleuglyleuhisvalproasngluleuglyleulysphe
195200205
cyslysargserpheservaltyrprothrleuasntrpaspthrser
210215220
lysileaspargleucyspheservalileserthraspprothrleu
225230235240
valproserseraspgluglyaspileglulysphehisasntyrala
245250255
thrlysalaprotyralatyrvalglyglulysargthrleuvaltyr
260265270
glyleuthrleuserprolysgluglutyrtyrlysleuglyalaval
275280285
tyrhisilethraspvalglnarglysleuleulysalapheaspser
290295300
leugluasp
305
<210>70
<211>1632
<212>dna
<213>大麻
<220>
<221>cds
<222>(1)..(1632)
<400>70
atggaaaagagtggctacggacgcgacggtatttaccgtagcctgcgt48
metglulysserglytyrglyargaspglyiletyrargserleuarg
151015
cctcctttacacctgccaaacaataacaatttgagtatggtctcattc96
proproleuhisleuproasnasnasnasnleusermetvalserphe
202530
ctgttccgtaacagcagcagctatccacagaaaccggcgttgatcgat144
leupheargasnsersersertyrproglnlysproalaleuileasp
354045
agcgagactaatcaaattttatcttttagtcattttaaaagcaccgtg192
sergluthrasnglnileleuserpheserhisphelysserthrval
505560
atcaaggtctcccatggcttcttaaacctggggatcaaaaagaatgac240
ilelysvalserhisglypheleuasnleuglyilelyslysasnasp
65707580
gtggttttaatctacgcacccaattcgatccactttcccgtatgcttc288
valvalleuiletyralaproasnserilehispheprovalcysphe
859095
cttggcattattgcttctggggcgatcgccactacttcaaatccatta336
leuglyileilealaserglyalailealathrthrserasnproleu
100105110
tacaccgtgagtgagttgtcgaaacaagtaaaggactcgaaccctaaa384
tyrthrvalsergluleuserlysglnvallysaspserasnprolys
115120125
ttgattatcacagtccctcagttattggaaaaggtcaagggtttcaat432
leuileilethrvalproglnleuleuglulysvallysglypheasn
130135140
ctgccaactatccttatcggccctgattctgagcaggaatcgtctagt480
leuprothrileleuileglyproaspsergluglngluserserser
145150155160
gataaagtaatgactttcaatgatctggtcaatctgggaggaagttcg528
asplysvalmetthrpheasnaspleuvalasnleuglyglyserser
165170175
ggtagcgaattccctatcgtcgacgatttcaagcaatccgacaccgcc576
glyserglupheproilevalaspaspphelysglnseraspthrala
180185190
gcactgttgtactcaagtggcacgacaggtatgagcaagggggtcgtt624
alaleuleutyrserserglythrthrglymetserlysglyvalval
195200205
ctgacgcacaaaaattttattgcctcatcgttgatggtaacaatggaa672
leuthrhislysasnpheilealaserserleumetvalthrmetglu
210215220
caggacttggtcggcgagatggacaatgtgttcctgtgtttccttcct720
glnaspleuvalglyglumetaspasnvalpheleucyspheleupro
225230235240
atgtttcacgtctttggcttagccattattacgtatgctcagttacag768
metphehisvalpheglyleualaileilethrtyralaglnleugln
245250255
cgcggtaataccgtgatttcaatggcccgctttgacttggaaaagatg816
argglyasnthrvalilesermetalaargpheaspleuglulysmet
260265270
ttaaaagatgttgaaaagtacaaagttacccacctttgggtcgtaccc864
leulysaspvalglulystyrlysvalthrhisleutrpvalvalpro
275280285
ccagttatcttagcgttgtcgaagaactcaatggtgaaaaaattcaat912
provalileleualaleuserlysasnsermetvallyslyspheasn
290295300
ttgtcatccatcaagtatattggttcaggcgctgcgccattaggaaag960
leuserserilelystyrileglyserglyalaalaproleuglylys
305310315320
gatctgatggaagaatgctctaaggtggttccttacggaatcgtggct1008
aspleumetgluglucysserlysvalvalprotyrglyilevalala
325330335
caaggatatggcatgacggaaacgtgcggaatcgtatccatggaagac1056
glnglytyrglymetthrgluthrcysglyilevalsermetgluasp
340345350
atccgcggcgggaaacgcaattcagggtcggccggaatgttggcaagt1104
ileargglyglylysargasnserglyseralaglymetleualaser
355360365
ggggtagaagctcagatcgtgagtgtggacaccttaaaaccccttccc1152
glyvalglualaglnilevalservalaspthrleulysproleupro
370375380
ccgaatcaattaggggaaatctgggtaaaaggtccaaatatgatgcaa1200
proasnglnleuglygluiletrpvallysglyproasnmetmetgln
385390395400
ggctatttcaacaatcctcaagcgaccaaacttaccattgataaaaag1248
glytyrpheasnasnproglnalathrlysleuthrileasplyslys
405410415
ggttgggttcatactggcgacttggggtatttcgacgaagacggacac1296
glytrpvalhisthrglyaspleuglytyrpheaspgluaspglyhis
420425430
ttatatgttgtagaccgtattaaggagcttattaaatacaagggattc1344
leutyrvalvalaspargilelysgluleuilelystyrlysglyphe
435440445
caagttgcgcctgcggaactggagggattattagttagtcaccccgag1392
glnvalalaproalagluleugluglyleuleuvalserhisproglu
450455460
atcttagacgcggtagttattcccttccccgatgctgaggcaggcgaa1440
ileleuaspalavalvalilepropheproaspalaglualaglyglu
465470475480
gtcccggtggcatacgttgttcgctcgcctaacagttcgttgaccgaa1488
valprovalalatyrvalvalargserproasnserserleuthrglu
485490495
aatgacgttaaaaaattcatcgccggtcaggtcgcctcctttaagcgt1536
asnaspvallyslyspheilealaglyglnvalalaserphelysarg
500505510
ctgcgcaaggttacttttattaattccgtccccaagagcgcaagtggg1584
leuarglysvalthrpheileasnservalprolysseralasergly
515520525
aagattctgcgccgcgagcttattcaaaaggttcgctctaacatgtaa1632
lysileleuargarggluleuileglnlysvalargserasnmet
530535540
<210>71
<211>543
<212>prt
<213>大麻
<400>71
metglulysserglytyrglyargaspglyiletyrargserleuarg
151015
proproleuhisleuproasnasnasnasnleusermetvalserphe
202530
leupheargasnsersersertyrproglnlysproalaleuileasp
354045
sergluthrasnglnileleuserpheserhisphelysserthrval
505560
ilelysvalserhisglypheleuasnleuglyilelyslysasnasp
65707580
valvalleuiletyralaproasnserilehispheprovalcysphe
859095
leuglyileilealaserglyalailealathrthrserasnproleu
100105110
tyrthrvalsergluleuserlysglnvallysaspserasnprolys
115120125
leuileilethrvalproglnleuleuglulysvallysglypheasn
130135140
leuprothrileleuileglyproaspsergluglngluserserser
145150155160
asplysvalmetthrpheasnaspleuvalasnleuglyglyserser
165170175
glyserglupheproilevalaspaspphelysglnseraspthrala
180185190
alaleuleutyrserserglythrthrglymetserlysglyvalval
195200205
leuthrhislysasnpheilealaserserleumetvalthrmetglu
210215220
glnaspleuvalglyglumetaspasnvalpheleucyspheleupro
225230235240
metphehisvalpheglyleualaileilethrtyralaglnleugln
245250255
argglyasnthrvalilesermetalaargpheaspleuglulysmet
260265270
leulysaspvalglulystyrlysvalthrhisleutrpvalvalpro
275280285
provalileleualaleuserlysasnsermetvallyslyspheasn
290295300
leuserserilelystyrileglyserglyalaalaproleuglylys
305310315320
aspleumetgluglucysserlysvalvalprotyrglyilevalala
325330335
glnglytyrglymetthrgluthrcysglyilevalsermetgluasp
340345350
ileargglyglylysargasnserglyseralaglymetleualaser
355360365
glyvalglualaglnilevalservalaspthrleulysproleupro
370375380
proasnglnleuglygluiletrpvallysglyproasnmetmetgln
385390395400
glytyrpheasnasnproglnalathrlysleuthrileasplyslys
405410415
glytrpvalhisthrglyaspleuglytyrpheaspgluaspglyhis
420425430
leutyrvalvalaspargilelysgluleuilelystyrlysglyphe
435440445
glnvalalaproalagluleugluglyleuleuvalserhisproglu
450455460
ileleuaspalavalvalilepropheproaspalaglualaglyglu
465470475480
valprovalalatyrvalvalargserproasnserserleuthrglu
485490495
asnaspvallyslyspheilealaglyglnvalalaserphelysarg
500505510
leuarglysvalthrpheileasnservalprolysseralasergly
515520525
lysileleuargarggluleuileglnlysvalargserasnmet
530535540
<210>72
<211>2163
<212>dna
<213>大麻
<220>
<221>cds
<222>(1)..(2163)
<400>72
atgggtaagaattacaagtccctggactctgttgtggcctctgacttc48
metglylysasntyrlysserleuaspservalvalalaseraspphe
151015
atagccctaggtatcacctctgaagttgctgagacactccatggtaga96
ilealaleuglyilethrsergluvalalagluthrleuhisglyarg
202530
ctggccgagatcgtgtgtaattatggcgctgccactccccaaacatgg144
leualagluilevalcysasntyrglyalaalathrproglnthrtrp
354045
atcaatattgccaaccatattctgtcgcctgacctccccttctccctg192
ileasnilealaasnhisileleuserproaspleupropheserleu
505560
caccagatgctcttctatggttgctataaagactttggacctgcccct240
hisglnmetleuphetyrglycystyrlysasppheglyproalapro
65707580
cctgcttggatacccgacccggagaaagtaaagtccaccaatctgggc288
proalatrpileproaspproglulysvallysserthrasnleugly
859095
gcacttttggagaagcgaggaaaagagtttttgggagtcaagtataag336
alaleuleuglulysargglylysglupheleuglyvallystyrlys
100105110
gatcccatttcaagcttttctcatttccaagaattttctgtaagaaac384
aspproileserserpheserhispheglnglupheservalargasn
115120125
cctgaggtgtattggagaacagtactaatggatgagatgaagataagt432
progluvaltyrtrpargthrvalleumetaspglumetlysileser
130135140
ttttcaaaggatccagaatgtatattgcgtagagatgatattaataat480
pheserlysaspproglucysileleuargargaspaspileasnasn
145150155160
ccagggggtagtgaatggcttccaggaggttatcttaactcagcaaag528
proglyglyserglutrpleuproglyglytyrleuasnseralalys
165170175
aattgcttgaatgtaaatagtaacaagaaattgaatgatacaatgatt576
asncysleuasnvalasnserasnlyslysleuasnaspthrmetile
180185190
gtatggcgtgatgaaggaaatgatgatttgcctctaaacaaattgaca624
valtrpargaspgluglyasnaspaspleuproleuasnlysleuthr
195200205
cttgaccaattgcgtaaacgtgtttggttagttggttatgcacttgaa672
leuaspglnleuarglysargvaltrpleuvalglytyralaleuglu
210215220
gaaatgggtttggagaagggttgtgcaattgcaattgatatgccaatg720
glumetglyleuglulysglycysalailealaileaspmetpromet
225230235240
catgtggatgctgtggttatctatctagctattgttcttgcgggatat768
hisvalaspalavalvaliletyrleualailevalleualaglytyr
245250255
gtagttgtttctattgctgatagtttttctgctcctgaaatatcaaca816
valvalvalserilealaaspserpheseralaprogluileserthr
260265270
agacttcgactatcaaaagcaaaagccatttttacacaggatcatatt864
argleuargleuserlysalalysalailephethrglnasphisile
275280285
attcgtgggaagaagcgtattcccttatacagtagagttgtggaagcc912
ileargglylyslysargileproleutyrserargvalvalgluala
290295300
aagtctcccatggccattgttattccttgtagtggctctaatattggt960
lysserprometalailevalileprocysserglyserasnilegly
305310315320
gcagaattgcgtgatggcgatatttcttgggattactttctagaaaga1008
alagluleuargaspglyaspilesertrpasptyrpheleugluarg
325330335
gcaaaagagtttaaaaattgtgaatttactgctagagaacaaccagtt1056
alalysgluphelysasncysgluphethralaarggluglnproval
340345350
gatgcctatacaaacatcctcttctcatctggaacaacaggggagcca1104
aspalatyrthrasnileleupheserserglythrthrglyglupro
355360365
aaggcaattccatggactcaagcaactcctttaaaagcagctgcagat1152
lysalaileprotrpthrglnalathrproleulysalaalaalaasp
370375380
gggtggagccatttggacattaggaaaggtgatgtcattgtttggccc1200
glytrpserhisleuaspilearglysglyaspvalilevaltrppro
385390395400
actaatcttggttggatgatgggtccttggctggtctatgcttcactc1248
thrasnleuglytrpmetmetglyprotrpleuvaltyralaserleu
405410415
cttaatggggcttctattgccttgtataatggatcaccacttgtttct1296
leuasnglyalaserilealaleutyrasnglyserproleuvalser
420425430
ggctttgccaaatttgtgcaggatgctaaagtaacaatgctaggtgtg1344
glyphealalysphevalglnaspalalysvalthrmetleuglyval
435440445
gtccctagtattgttcgatcatggaaaagtaccaattgtgttagtggc1392
valproserilevalargsertrplysserthrasncysvalsergly
450455460
tatgattggtccaccatccgttgcttttcctcttctggtgaagcatct1440
tyrasptrpserthrileargcyspheserserserglyglualaser
465470475480
aatgtagatgaatacctatggttgatggggagagcaaactacaagcct1488
asnvalaspglutyrleutrpleumetglyargalaasntyrlyspro
485490495
gttatcgaaatgtgtggtggcacagaaattggtggtgcattttctgct1536
valileglumetcysglyglythrgluileglyglyalapheserala
500505510
ggctctttcttacaagctcaatcattatcttcatttagttcacaatgt1584
glyserpheleuglnalaglnserleuserserpheserserglncys
515520525
atgggttgcactttatacatacttgacaagaatggttatccaatgcct1632
metglycysthrleutyrileleuasplysasnglytyrprometpro
530535540
aaaaacaaaccaggaattggtgaattagcgcttggtccagtcatgttt1680
lysasnlysproglyileglygluleualaleuglyprovalmetphe
545550555560
ggagcatcgaagactctgttgaatggtaatcaccatgatgtttatttt1728
glyalaserlysthrleuleuasnglyasnhishisaspvaltyrphe
565570575
aagggaatgcctacattgaatggagaggttttaaggaggcatggggac1776
lysglymetprothrleuasnglygluvalleuargarghisglyasp
580585590
atttttgagcttacatctaatggttattatcatgcacatggtcgtgca1824
ilephegluleuthrserasnglytyrtyrhisalahisglyargala
595600605
gatgatacaatgaatattggaggcatcaagattagttccatagagatt1872
aspaspthrmetasnileglyglyilelysileserserilegluile
610615620
gaacgagtttgtaatgaagttgatgacagagttttcgagacaactgct1920
gluargvalcysasngluvalaspaspargvalphegluthrthrala
625630635640
attggagtgccacctttgggcggtggacctgagcaattagtaattttc1968
ileglyvalproproleuglyglyglyprogluglnleuvalilephe
645650655
tttgtattaaaagattcaaatgatacaactattgacttaaatcaattg2016
phevalleulysaspserasnaspthrthrileaspleuasnglnleu
660665670
aggttatctttcaacttgggtttacagaagaaactaaatcctctgttc2064
argleuserpheasnleuglyleuglnlyslysleuasnproleuphe
675680685
aaggtcactcgtgttgtgcctctttcatcacttccgagaacagcaacc2112
lysvalthrargvalvalproleuserserleuproargthralathr
690695700
aacaagatcatgagaagggttttgcgccagcaattttctcactttgaa2160
asnlysilemetargargvalleuargglnglnpheserhispheglu
705710715720
tga2163
<210>73
<211>720
<212>prt
<213>大麻
<400>73
metglylysasntyrlysserleuaspservalvalalaseraspphe
151015
ilealaleuglyilethrsergluvalalagluthrleuhisglyarg
202530
leualagluilevalcysasntyrglyalaalathrproglnthrtrp
354045
ileasnilealaasnhisileleuserproaspleupropheserleu
505560
hisglnmetleuphetyrglycystyrlysasppheglyproalapro
65707580
proalatrpileproaspproglulysvallysserthrasnleugly
859095
alaleuleuglulysargglylysglupheleuglyvallystyrlys
100105110
aspproileserserpheserhispheglnglupheservalargasn
115120125
progluvaltyrtrpargthrvalleumetaspglumetlysileser
130135140
pheserlysaspproglucysileleuargargaspaspileasnasn
145150155160
proglyglyserglutrpleuproglyglytyrleuasnseralalys
165170175
asncysleuasnvalasnserasnlyslysleuasnaspthrmetile
180185190
valtrpargaspgluglyasnaspaspleuproleuasnlysleuthr
195200205
leuaspglnleuarglysargvaltrpleuvalglytyralaleuglu
210215220
glumetglyleuglulysglycysalailealaileaspmetpromet
225230235240
hisvalaspalavalvaliletyrleualailevalleualaglytyr
245250255
valvalvalserilealaaspserpheseralaprogluileserthr
260265270
argleuargleuserlysalalysalailephethrglnasphisile
275280285
ileargglylyslysargileproleutyrserargvalvalgluala
290295300
lysserprometalailevalileprocysserglyserasnilegly
305310315320
alagluleuargaspglyaspilesertrpasptyrpheleugluarg
325330335
alalysgluphelysasncysgluphethralaarggluglnproval
340345350
aspalatyrthrasnileleupheserserglythrthrglyglupro
355360365
lysalaileprotrpthrglnalathrproleulysalaalaalaasp
370375380
glytrpserhisleuaspilearglysglyaspvalilevaltrppro
385390395400
thrasnleuglytrpmetmetglyprotrpleuvaltyralaserleu
405410415
leuasnglyalaserilealaleutyrasnglyserproleuvalser
420425430
glyphealalysphevalglnaspalalysvalthrmetleuglyval
435440445
valproserilevalargsertrplysserthrasncysvalsergly
450455460
tyrasptrpserthrileargcyspheserserserglyglualaser
465470475480
asnvalaspglutyrleutrpleumetglyargalaasntyrlyspro
485490495
valileglumetcysglyglythrgluileglyglyalapheserala
500505510
glyserpheleuglnalaglnserleuserserpheserserglncys
515520525
metglycysthrleutyrileleuasplysasnglytyrprometpro
530535540
lysasnlysproglyileglygluleualaleuglyprovalmetphe
545550555560
glyalaserlysthrleuleuasnglyasnhishisaspvaltyrphe
565570575
lysglymetprothrleuasnglygluvalleuargarghisglyasp
580585590
ilephegluleuthrserasnglytyrtyrhisalahisglyargala
595600605
aspaspthrmetasnileglyglyilelysileserserilegluile
610615620
gluargvalcysasngluvalaspaspargvalphegluthrthrala
625630635640
ileglyvalproproleuglyglyglyprogluglnleuvalilephe
645650655
phevalleulysaspserasnaspthrthrileaspleuasnglnleu
660665670
argleuserpheasnleuglyleuglnlyslysleuasnproleuphe
675680685
lysvalthrargvalvalproleuserserleuproargthralathr
690695700
asnlysilemetargargvalleuargglnglnpheserhispheglu
705710715720
<210>74
<211>1695
<212>dna
<213>大麻
<220>
<221>cds
<222>(1)..(1695)
<400>74
atggaagtactgaaggaggttgcgaaggaaggtagcgcagcccgtgaa48
metgluvalleulysgluvalalalysgluglyseralaalaargglu
151015
ggtgtcgctattcgcgccgaccagaaatcgtacagctataagcaattg96
glyvalalaileargalaaspglnlyssertyrsertyrlysglnleu
202530
atctcctccgcgcagtcgatctgctcactgttatgcggtactgaactt144
ileserseralaglnserilecysserleuleucysglythrgluleu
354045
aaagcgattcacgaagccgggaaacaagctcgtcctagcgcgtctatc192
lysalailehisglualaglylysglnalaargproseralaserile
505560
aatggggccgggggtcacggccacttgggaggagctcgtattggaatt240
asnglyalaglyglyhisglyhisleuglyglyalaargileglyile
65707580
gttgctaagccgtcggcagaatttgtagccggtgttttaggtacgtgg288
valalalysproseralagluphevalalaglyvalleuglythrtrp
859095
ttatctggtggagttgcggttccccttgcactgtcttacccggaggcg336
leuserglyglyvalalavalproleualaleusertyrprogluala
100105110
gaattactgcatgtcatgaacgattcagatatcagcatgatcttgagc384
gluleuleuhisvalmetasnaspseraspilesermetileleuser
115120125
acggaagaccatcaagaactgatgcaaaatattgctgccaagacttcc432
thrgluasphisglngluleumetglnasnilealaalalysthrser
130135140
gcacagttttccttaattccatctgtgccgtcgtcgtgctcacaagaa480
alaglnpheserleuileproservalprosersercysserglnglu
145150155160
gtagcggtcgatcatcgtcagaccggtgacatctctaccgactctatc528
valalavalasphisargglnthrglyaspileserthraspserile
165170175
ttgcttaaccgcgagatctctaacgagaatcccgcacttatcgtctat576
leuleuasnarggluileserasngluasnproalaleuilevaltyr
180185190
acgtcggggacgacaggcaagccgaagggcgtcgttcacacacaccaa624
thrserglythrthrglylysprolysglyvalvalhisthrhisgln
195200205
tcaatttctgcacaggttcagacgttagccaaggcatgggagtatact672
serileseralaglnvalglnthrleualalysalatrpglutyrthr
210215220
cctgccgatcaattcttacactgcttaccgctgcatcatgtgcatggg720
proalaaspglnpheleuhiscysleuproleuhishisvalhisgly
225230235240
ctgtttaacgcactgttcgcgcccctttacgcgcgttcaacagttgaa768
leupheasnalaleuphealaproleutyralaargserthrvalglu
245250255
tttctgccgaaattttctgtccgcggtatttggcaacgctggcgcgaa816
pheleuprolyspheservalargglyiletrpglnargtrpargglu
260265270
tcctacccaacgtcagagacgaaagccaatgactgcattacggtattt864
sertyrprothrsergluthrlysalaasnaspcysilethrvalphe
275280285
acaggagttcccaccatgtacacgcgtctgattcaaggatatgaagct912
thrglyvalprothrmettyrthrargleuileglnglytyrgluala
290295300
atggatccagagttaaaagaggcctctgcatctgctgctaagcagctg960
metaspprogluleulysglualaseralaseralaalalysglnleu
305310315320
cgccttatgatgtgtggttcctctgcgctgccagttcctgtcatgcag1008
argleumetmetcysglyserseralaleuprovalprovalmetgln
325330335
cagtggcaaaccatcaccggccaccgtcttctggaacgttacggaatg1056
glntrpglnthrilethrglyhisargleuleugluargtyrglymet
340345350
accgaatttgtcatggcaatttctaaccccttgaaaggtgagcgcaaa1104
thrgluphevalmetalaileserasnproleulysglygluarglys
355360365
tccggtactgtcggaaagccgtttccaggtgtagaggtgcgcatttta1152
serglythrvalglylyspropheproglyvalgluvalargileleu
370375380
gcagaggatgaaaacggcgatgatgctaccggggtgggagagctgtgc1200
alagluaspgluasnglyaspaspalathrglyvalglygluleucys
385390395400
gtacgcagtccgtcccttttcaaagagtattggcgtttgcccgaggtc1248
valargserproserleuphelysglutyrtrpargleuprogluval
405410415
acaaaagcctcctttacagacgacggctttttcaaaaccggcgacgca1296
thrlysalaserphethraspaspglyphephelysthrglyaspala
420425430
ggcaaggtcgatgaggacggttactacgtgattctgggccgtactagc1344
glylysvalaspgluaspglytyrtyrvalileleuglyargthrser
435440445
gcagatattatgaaagttggaggctataagctgtctgctctggaaatc1392
alaaspilemetlysvalglyglytyrlysleuseralaleugluile
450455460
gagtcggtccttctggaacacccgactgtcgaggaatgctgtgtcttg1440
gluservalleuleugluhisprothrvalgluglucyscysvalleu
465470475480
ggacttcccgacaaggattatggggaagccgtatccgcaatcattgta1488
glyleuproasplysasptyrglyglualavalseralaileileval
485490495
ccggcagccgaggcgaagaagaaacgcgaagaggagtcacgccccgcc1536
proalaalaglualalyslyslysarggluglugluserargproala
500505510
attagtctggaggaactgttctcatgggcacagcacaaacttgccccc1584
ileserleuglugluleuphesertrpalaglnhislysleualapro
515520525
tacaaactgcccacgcgtttattcctgtgggactctttacctcgcaac1632
tyrlysleuprothrargleupheleutrpaspserleuproargasn
530535540
gcaatggggaaagtcaacaaaaaagagctgaagaaaaaactgacagtt1680
alametglylysvalasnlyslysgluleulyslyslysleuthrval
545550555560
gagcaaggtatttaa1695
gluglnglyile
<210>75
<211>564
<212>prt
<213>大麻
<400>75
metgluvalleulysgluvalalalysgluglyseralaalaargglu
151015
glyvalalaileargalaaspglnlyssertyrsertyrlysglnleu
202530
ileserseralaglnserilecysserleuleucysglythrgluleu
354045
lysalailehisglualaglylysglnalaargproseralaserile
505560
asnglyalaglyglyhisglyhisleuglyglyalaargileglyile
65707580
valalalysproseralagluphevalalaglyvalleuglythrtrp
859095
leuserglyglyvalalavalproleualaleusertyrprogluala
100105110
gluleuleuhisvalmetasnaspseraspilesermetileleuser
115120125
thrgluasphisglngluleumetglnasnilealaalalysthrser
130135140
alaglnpheserleuileproservalprosersercysserglnglu
145150155160
valalavalasphisargglnthrglyaspileserthraspserile
165170175
leuleuasnarggluileserasngluasnproalaleuilevaltyr
180185190
thrserglythrthrglylysprolysglyvalvalhisthrhisgln
195200205
serileseralaglnvalglnthrleualalysalatrpglutyrthr
210215220
proalaaspglnpheleuhiscysleuproleuhishisvalhisgly
225230235240
leupheasnalaleuphealaproleutyralaargserthrvalglu
245250255
pheleuprolyspheservalargglyiletrpglnargtrpargglu
260265270
sertyrprothrsergluthrlysalaasnaspcysilethrvalphe
275280285
thrglyvalprothrmettyrthrargleuileglnglytyrgluala
290295300
metaspprogluleulysglualaseralaseralaalalysglnleu
305310315320
argleumetmetcysglyserseralaleuprovalprovalmetgln
325330335
glntrpglnthrilethrglyhisargleuleugluargtyrglymet
340345350
thrgluphevalmetalaileserasnproleulysglygluarglys
355360365
serglythrvalglylyspropheproglyvalgluvalargileleu
370375380
alagluaspgluasnglyaspaspalathrglyvalglygluleucys
385390395400
valargserproserleuphelysglutyrtrpargleuprogluval
405410415
thrlysalaserphethraspaspglyphephelysthrglyaspala
420425430
glylysvalaspgluaspglytyrtyrvalileleuglyargthrser
435440445
alaaspilemetlysvalglyglytyrlysleuseralaleugluile
450455460
gluservalleuleugluhisprothrvalgluglucyscysvalleu
465470475480
glyleuproasplysasptyrglyglualavalseralaileileval
485490495
proalaalaglualalyslyslysarggluglugluserargproala
500505510
ileserleuglugluleuphesertrpalaglnhislysleualapro
515520525
tyrlysleuprothrargleupheleutrpaspserleuproargasn
530535540
alametglylysvalasnlyslysgluleulyslyslysleuthrval
545550555560
gluglnglyile
<210>76
<211>1158
<212>dna
<213>大麻
<220>
<221>cds
<222>(1)..(1158)
<400>76
atgaatcatctgcgtgctgaaggaccagcttccgtattggcaattgga48
metasnhisleuargalagluglyproalaservalleualailegly
151015
acagctaaccctgagaacattcttcttcaggatgagtttcccgactat96
thralaasnprogluasnileleuleuglnaspglupheproasptyr
202530
tacttccgcgtgacaaagagcgaacacatgacacagcttaaagagaag144
tyrpheargvalthrlyssergluhismetthrglnleulysglulys
354045
ttccgtaagatctgtgacaaaagcatgatccgcaaacgtaactgcttc192
phearglysilecysasplyssermetilearglysargasncysphe
505560
cttaacgaggagcatctgaagcagaatccccgtcttgttgaacatgag240
leuasnglugluhisleulysglnasnproargleuvalgluhisglu
65707580
atgcagaccttggatgctcgccaggacatgttggttgttgaggtccct288
metglnthrleuaspalaargglnaspmetleuvalvalgluvalpro
859095
aagctgggcaaagatgcgtgtgcaaaagcgattaaagagtgggggcag336
lysleuglylysaspalacysalalysalailelysglutrpglygln
100105110
cctaaaagcaaaattactcatctgattttcacaagcgccagtacaacc384
prolysserlysilethrhisleuilephethrseralaserthrthr
115120125
gatatgcccggtgcggactaccattgtgcaaaattattgggtttatcg432
aspmetproglyalaasptyrhiscysalalysleuleuglyleuser
130135140
ccttcagtaaaacgtgttatgatgtaccagttaggatgctacggtggt480
proservallysargvalmetmettyrglnleuglycystyrglygly
145150155160
ggcaccgtacttcgtattgcgaaggacatcgccgagaacaacaaagga528
glythrvalleuargilealalysaspilealagluasnasnlysgly
165170175
gcccgtgtacttgctgtatgttgtgatatcatggcgtgcctttttcgc576
alaargvalleualavalcyscysaspilemetalacysleuphearg
180185190
ggccccagcgagagtgaccttgagttacttgtggggcaggccatcttc624
glyprosergluseraspleugluleuleuvalglyglnalailephe
195200205
ggagacggtgccgcagccgtcattgttggcgcagagcccgatgaatcc672
glyaspglyalaalaalavalilevalglyalagluproaspgluser
210215220
gttggcgagcgcccgatctttgagcttgtaagtacaggacaaactatc720
valglygluargproilephegluleuvalserthrglyglnthrile
225230235240
ttgcccaactctgaggggactatcggcggacatattcgtgaggcgggc768
leuproasnsergluglythrileglyglyhisileargglualagly
245250255
ttgatttttgaccttcacaaggatgttccaatgcttatctccaataat816
leuilepheaspleuhislysaspvalprometleuileserasnasn
260265270
attgaaaaatgtcttatcgaagcattcactccgattggtatctccgat864
ileglulyscysleuileglualaphethrproileglyileserasp
275280285
tggaattcgattttttggatcacccatcctggtgggaaagctatttta912
trpasnserilephetrpilethrhisproglyglylysalaileleu
290295300
gacaaggtggaggagaaattacatcttaagtcagataagtttgtcgac960
asplysvalgluglulysleuhisleulysserasplysphevalasp
305310315320
agtcgccacgtgttgtcggaacatggcaacatgtcatcgtcaaccgtc1008
serarghisvalleusergluhisglyasnmetserserserthrval
325330335
ttgttcgttatggacgaattacgtaaacgcagtttagaagagggtaag1056
leuphevalmetaspgluleuarglysargserleuglugluglylys
340345350
agtacgacgggggacgggttcgagtggggagtcttattcgggttcggt1104
serthrthrglyaspglypheglutrpglyvalleupheglyphegly
355360365
ccaggattgacagtggaacgcgtcgtggttcgcagtgtccccattaag1152
proglyleuthrvalgluargvalvalvalargservalproilelys
370375380
tactaa1158
tyr
385
<210>77
<211>385
<212>prt
<213>大麻
<400>77
metasnhisleuargalagluglyproalaservalleualailegly
151015
thralaasnprogluasnileleuleuglnaspglupheproasptyr
202530
tyrpheargvalthrlyssergluhismetthrglnleulysglulys
354045
phearglysilecysasplyssermetilearglysargasncysphe
505560
leuasnglugluhisleulysglnasnproargleuvalgluhisglu
65707580
metglnthrleuaspalaargglnaspmetleuvalvalgluvalpro
859095
lysleuglylysaspalacysalalysalailelysglutrpglygln
100105110
prolysserlysilethrhisleuilephethrseralaserthrthr
115120125
aspmetproglyalaasptyrhiscysalalysleuleuglyleuser
130135140
proservallysargvalmetmettyrglnleuglycystyrglygly
145150155160
glythrvalleuargilealalysaspilealagluasnasnlysgly
165170175
alaargvalleualavalcyscysaspilemetalacysleuphearg
180185190
glyprosergluseraspleugluleuleuvalglyglnalailephe
195200205
glyaspglyalaalaalavalilevalglyalagluproaspgluser
210215220
valglygluargproilephegluleuvalserthrglyglnthrile
225230235240
leuproasnsergluglythrileglyglyhisileargglualagly
245250255
leuilepheaspleuhislysaspvalprometleuileserasnasn
260265270
ileglulyscysleuileglualaphethrproileglyileserasp
275280285
trpasnserilephetrpilethrhisproglyglylysalaileleu
290295300
asplysvalgluglulysleuhisleulysserasplysphevalasp
305310315320
serarghisvalleusergluhisglyasnmetserserserthrval
325330335
leuphevalmetaspgluleuarglysargserleuglugluglylys
340345350
serthrthrglyaspglypheglutrpglyvalleupheglyphegly
355360365
proglyleuthrvalgluargvalvalvalargservalproilelys
370375380
tyr
385
<210>78
<211>306
<212>dna
<213>大麻
<220>
<221>cds
<222>(1)..(306)
<400>78
atggcagtcaaacacttgatcgtgttaaagttcaaagatgaaatcaca48
metalavallyshisleuilevalleulysphelysaspgluilethr
151015
gaggctcagaaggaagaatttttcaagacgtatgtaaaccttgttaat96
glualaglnlysglugluphephelysthrtyrvalasnleuvalasn
202530
atcatccccgctatgaaggatgtgtattggggtaaagacgtgacacag144
ileileproalametlysaspvaltyrtrpglylysaspvalthrgln
354045
aagaacaaagaggaaggctacacgcacatcgtagaggtcacatttgag192
lysasnlysglugluglytyrthrhisilevalgluvalthrpheglu
505560
agcgtcgaaactattcaggattacatcattcatcccgcacacgttgga240
servalgluthrileglnasptyrileilehisproalahisvalgly
65707580
ttcggggatgtgtatcgctctttctgggaaaaattgctgatcttcgac288
pheglyaspvaltyrargserphetrpglulysleuleuilepheasp
859095
tatacaccgcgtaagtaa306
tyrthrproarglys
100
<210>79
<211>101
<212>prt
<213>大麻
<400>79
metalavallyshisleuilevalleulysphelysaspgluilethr
151015
glualaglnlysglugluphephelysthrtyrvalasnleuvalasn
202530
ileileproalametlysaspvaltyrtrpglylysaspvalthrgln
354045
lysasnlysglugluglytyrthrhisilevalgluvalthrpheglu
505560
servalgluthrileglnasptyrileilehisproalahisvalgly
65707580
pheglyaspvaltyrargserphetrpglulysleuleuilepheasp
859095
tyrthrproarglys
100
<210>80
<211>654
<212>dna
<213>嗜热脱氮土芽孢杆菌
<220>
<221>cds
<222>(1)..(654)
<400>80
atgaatttagtgctgatggggctgccaggtgccggcaaaggcacgcaa48
metasnleuvalleumetglyleuproglyalaglylysglythrgln
151015
gccgagaaaatcgtagaaacatatggaatcccacatatttcaaccggg96
alaglulysilevalgluthrtyrglyileprohisileserthrgly
202530
gatatgtttcgggcggcgatgaaagaaggcacaccgttaggattgcag144
aspmetpheargalaalametlysgluglythrproleuglyleugln
354045
gcaaaagaatatatcgaccgtggtgatcttgttccggatgaggtgacg192
alalysglutyrileaspargglyaspleuvalproaspgluvalthr
505560
atcggtatcgtccgtgaacggttaagcaaagacgactgccaaaacggc240
ileglyilevalarggluargleuserlysaspaspcysglnasngly
65707580
tttttgcttgacggattcccacgcacggttgcccaagcggaggcgctg288
pheleuleuaspglypheproargthrvalalaglnalaglualaleu
859095
gaagcgatgctggctgaaatcggccgcaagcttgactatgtcatccat336
glualametleualagluileglyarglysleuasptyrvalilehis
100105110
atcgatgttcgccaagatgtgttaatggagcgcctcacaggcagacga384
ileaspvalargglnaspvalleumetgluargleuthrglyargarg
115120125
atttgtcgcaactgcggagcgacataccatcttgtttttcacccaccg432
ilecysargasncysglyalathrtyrhisleuvalphehispropro
130135140
gctcagccaggcgtatgtgataaatgcggtggcgagctttatcagcgc480
alaglnproglyvalcysasplyscysglyglygluleutyrglnarg
145150155160
cctgacgataatgaagcaacagtggcgaatcggcttgaggtgaatacg528
proaspaspasnglualathrvalalaasnargleugluvalasnthr
165170175
aaacaaatgaagccattgctcgatttctatgagcaaaaaggctatttg576
lysglnmetlysproleuleuaspphetyrgluglnlysglytyrleu
180185190
cgtcacattaacggcgaacaagaaatggaaaaagtgtttagcgacatt624
arghisileasnglygluglnglumetglulysvalpheseraspile
195200205
cgcgaattgctcgggggacttactcgataa654
arggluleuleuglyglyleuthrarg
210215
<210>81
<211>217
<212>prt
<213>嗜热脱氮土芽孢杆菌
<400>81
metasnleuvalleumetglyleuproglyalaglylysglythrgln
151015
alaglulysilevalgluthrtyrglyileprohisileserthrgly
202530
aspmetpheargalaalametlysgluglythrproleuglyleugln
354045
alalysglutyrileaspargglyaspleuvalproaspgluvalthr
505560
ileglyilevalarggluargleuserlysaspaspcysglnasngly
65707580
pheleuleuaspglypheproargthrvalalaglnalaglualaleu
859095
glualametleualagluileglyarglysleuasptyrvalilehis
100105110
ileaspvalargglnaspvalleumetgluargleuthrglyargarg
115120125
ilecysargasncysglyalathrtyrhisleuvalphehispropro
130135140
alaglnproglyvalcysasplyscysglyglygluleutyrglnarg
145150155160
proaspaspasnglualathrvalalaasnargleugluvalasnthr
165170175
lysglnmetlysproleuleuaspphetyrgluglnlysglytyrleu
180185190
arghisileasnglygluglnglumetglulysvalpheseraspile
195200205
arggluleuleuglyglyleuthrarg
210215
<210>82
<211>1512
<212>dna
<213>沼泽红假单胞菌
<220>
<221>cds
<222>(1)..(1512)
<400>82
atgaacgccaacctgttcgcccgcctgttcgataagctcgacgacccc48
metasnalaasnleuphealaargleupheasplysleuaspasppro
151015
cacaagctcgcgatcgaaaccgcggccggggacaagatcagctacgcc96
hislysleualailegluthralaalaglyasplysilesertyrala
202530
gagctggtggcgcgggcgggccgcgtcgccaacgtgctggtggcacgc144
gluleuvalalaargalaglyargvalalaasnvalleuvalalaarg
354045
ggcctgcaggtcggcgaccgcgttgcggcgcaaaccgagaagtcggtg192
glyleuglnvalglyaspargvalalaalaglnthrglulysserval
505560
gaagcgctggtgctgtatctcgccacggtgcgggccggcggcgtgtat240
glualaleuvalleutyrleualathrvalargalaglyglyvaltyr
65707580
ctgccgctcaacaccgcctatacgctgcacgagctcgattacttcatc288
leuproleuasnthralatyrthrleuhisgluleuasptyrpheile
859095
accgatgccgagccgaagatcgtggtgtgcgatccgtccaagcgcgac336
thraspalagluprolysilevalvalcysaspproserlysargasp
100105110
gggatcgcggcgattgccgccaaggtcggcgccacggtggagacgctt384
glyilealaalailealaalalysvalglyalathrvalgluthrleu
115120125
ggccccgacggtcggggctcgctcaccgatgcggcagctggagccagc432
glyproaspglyargglyserleuthraspalaalaalaglyalaser
130135140
gaggcgttcgccacgatcgaccgcggcgccgatgatctggcggcgatc480
glualaphealathrileaspargglyalaaspaspleualaalaile
145150155160
ctctacacctcagggacgaccggccgctccaagggcgcgatgctcagc528
leutyrthrserglythrthrglyargserlysglyalametleuser
165170175
cacgacaatttggcgtcgaactcgctgacgctggtcgattactggcgc576
hisaspasnleualaserasnserleuthrleuvalasptyrtrparg
180185190
ttcacgccggatgacgtgctgatccacgcgctgccgatctatcacacc624
phethrproaspaspvalleuilehisalaleuproiletyrhisthr
195200205
catggattgttcgtggccagcaacgtcacgctgttcgcgcgcggatcg672
hisglyleuphevalalaserasnvalthrleuphealaargglyser
210215220
atgatcttcctgccgaagttcgatcccgacaagatcctcgacctgatg720
metilepheleuprolyspheaspproasplysileleuaspleumet
225230235240
gcgcgcgccaccgtgctgatgggtgtgccgacgttctacacgcggctc768
alaargalathrvalleumetglyvalprothrphetyrthrargleu
245250255
ttgcagagcccgcggctgaccaaggagacgacgggccacatgaggctg816
leuglnserproargleuthrlysgluthrthrglyhismetargleu
260265270
ttcatctccgggtcggcgccgctgctcgccgatacgcatcgcgaatgg864
pheileserglyseralaproleuleualaaspthrhisargglutrp
275280285
tcggcgaagaccggtcacgccgtgctcgagcgctacggcatgaccgag912
seralalysthrglyhisalavalleugluargtyrglymetthrglu
290295300
accaacatgaacacctcgaacccgtatgacggcgaccgcgtccccggc960
thrasnmetasnthrserasnprotyraspglyaspargvalprogly
305310315320
gcggtcggcccggcgctgcccggcgtttcggcgcgcgtgaccgatccg1008
alavalglyproalaleuproglyvalseralaargvalthrasppro
325330335
gaaaccggcaaggaactgccgcgcggcgacatcgggatgatcgaggtg1056
gluthrglylysgluleuproargglyaspileglymetilegluval
340345350
aagggcccgaacgtgttcaagggctactggcggatgccggagaagacc1104
lysglyproasnvalphelysglytyrtrpargmetproglulysthr
355360365
aagtctgaattccgcgacgacggcttcttcatcaccggcgacctcggc1152
lysserglupheargaspaspglyphepheilethrglyaspleugly
370375380
aagatcgacgagcgcggctacgtccacatcctcggccgcggcaaggat1200
lysileaspgluargglytyrvalhisileleuglyargglylysasp
385390395400
ctggtgatcaccggcggcttcaacgtctatccgaaggaaatcgagagc1248
leuvalilethrglyglypheasnvaltyrprolysgluilegluser
405410415
gagatcgacgccatgccgggcgtggtcgaatccgcggtgatcggcgtg1296
gluileaspalametproglyvalvalgluseralavalileglyval
420425430
ccgcacgccgatttcggcgagggcgtcactgccgtggtggtgcgcgac1344
prohisalaasppheglygluglyvalthralavalvalvalargasp
435440445
aagggtgccacgatcgacgaagcgcaggtgctgcacggcctcgacggt1392
lysglyalathrileaspglualaglnvalleuhisglyleuaspgly
450455460
cagctcgccaagttcaagatgccgaagaaagtgatcttcgtcgacgac1440
glnleualalysphelysmetprolyslysvalilephevalaspasp
465470475480
ctgccgcgcaacaccatgggcaaggtccagaagaacgtcctgcgcgag1488
leuproargasnthrmetglylysvalglnlysasnvalleuargglu
485490495
acctacaaggacatctacaagtaa1512
thrtyrlysaspiletyrlys
500
<210>83
<211>503
<212>prt
<213>沼泽红假单胞菌
<400>83
metasnalaasnleuphealaargleupheasplysleuaspasppro
151015
hislysleualailegluthralaalaglyasplysilesertyrala
202530
gluleuvalalaargalaglyargvalalaasnvalleuvalalaarg
354045
glyleuglnvalglyaspargvalalaalaglnthrglulysserval
505560
glualaleuvalleutyrleualathrvalargalaglyglyvaltyr
65707580
leuproleuasnthralatyrthrleuhisgluleuasptyrpheile
859095
thraspalagluprolysilevalvalcysaspproserlysargasp
100105110
glyilealaalailealaalalysvalglyalathrvalgluthrleu
115120125
glyproaspglyargglyserleuthraspalaalaalaglyalaser
130135140
glualaphealathrileaspargglyalaaspaspleualaalaile
145150155160
leutyrthrserglythrthrglyargserlysglyalametleuser
165170175
hisaspasnleualaserasnserleuthrleuvalasptyrtrparg
180185190
phethrproaspaspvalleuilehisalaleuproiletyrhisthr
195200205
hisglyleuphevalalaserasnvalthrleuphealaargglyser
210215220
metilepheleuprolyspheaspproasplysileleuaspleumet
225230235240
alaargalathrvalleumetglyvalprothrphetyrthrargleu
245250255
leuglnserproargleuthrlysgluthrthrglyhismetargleu
260265270
pheileserglyseralaproleuleualaaspthrhisargglutrp
275280285
seralalysthrglyhisalavalleugluargtyrglymetthrglu
290295300
thrasnmetasnthrserasnprotyraspglyaspargvalprogly
305310315320
alavalglyproalaleuproglyvalseralaargvalthrasppro
325330335
gluthrglylysgluleuproargglyaspileglymetilegluval
340345350
lysglyproasnvalphelysglytyrtrpargmetproglulysthr
355360365
lysserglupheargaspaspglyphepheilethrglyaspleugly
370375380
lysileaspgluargglytyrvalhisileleuglyargglylysasp
385390395400
leuvalilethrglyglypheasnvaltyrprolysgluilegluser
405410415
gluileaspalametproglyvalvalgluseralavalileglyval
420425430
prohisalaasppheglygluglyvalthralavalvalvalargasp
435440445
lysglyalathrileaspglualaglnvalleuhisglyleuaspgly
450455460
glnleualalysphelysmetprolyslysvalilephevalaspasp
465470475480
leuproargasnthrmetglylysvalglnlysasnvalleuargglu
485490495
thrtyrlysaspiletyrlys
500
- 还没有人留言评论。精彩留言会获得点赞!