一种基于代谢组学的代谢物组合模型的数据迭代处理方法
本发明涉及代谢组学与代谢物模型数据处理领域,具体涉及一种基于代谢组学的代谢物组合模型的数据迭代处理方法。
背景技术:
1、代谢组学是一门对某一生物或细胞所有低分子质量代谢产物(以相对分子质量<1000的有机和无机的代谢物为研究核心区)进行分析的新兴学科。生物样本通过nmr、gc-ms、lc-ms等高通量仪器分析检测后,能产生大量的数据,这些数据具有高维,少样本、高噪声等复杂特征,同时代谢物多且代谢物之间联系密切,因此从复杂的代谢组学数据中确定与所研究的现象有关的代谢物,并稳定进行产物与模型的协同迭代调整成为亟需解决的问题。
技术实现思路
1、针对现有技术的不足,本发明提供了一种基于代谢组学的代谢物组合模型的数据迭代处理方法,通过代谢组学及其延展模型,实现多种酶数据及通路图的协同调整数据迭代。
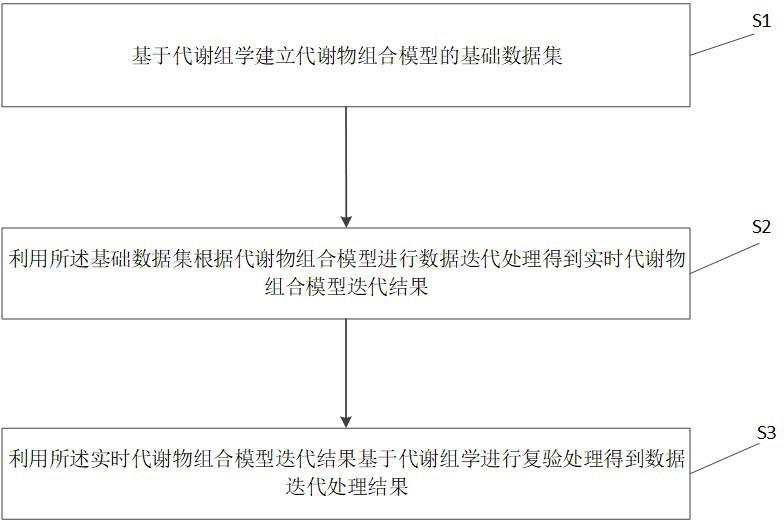
2、为实现上述目的,本发明提供了一种基于代谢组学的代谢物组合模型的数据迭代处理方法,包括:
3、s1、基于代谢组学建立代谢物组合模型的基础数据集;
4、s2、利用所述基础数据集根据代谢物组合模型进行数据迭代处理得到实时代谢物组合模型迭代结果;
5、s3、利用所述实时代谢物组合模型迭代结果基于代谢组学进行复验处理得到数据迭代处理结果。
6、优选的,所述基于代谢组学建立代谢物组合模型的基础数据集包括:
7、获取代谢物组合模型对应特征作为代谢物组合模型基准特征;
8、根据所述代谢物组合模型基准特征获取对应关联代谢物数据;
9、利用所述关联代谢物数据建立代谢物组合模型的基础数据集;
10、其中,所述关联代谢物数据包括当前时刻的代谢物种类与含量。
11、进一步的,利用所述基础数据集根据代谢物组合模型进行数据迭代处理得到实时代谢物组合模型迭代结果包括:
12、s2-1、利用所述基础数据集内各子集建立基础数据关联映射;
13、s2-2、利用所述基础数据关联映射作为迭代基准根据代谢物组合模型进行数据迭代处理得到实时代谢物组合模型迭代结果;
14、其中,所述基础数据关联映射为单一性映射。
15、进一步的,利用所述基础数据关联映射作为迭代基准根据代谢物组合模型进行数据迭代处理得到实时代谢物组合模型迭代结果包括:
16、s2-2-1、获取基础数据关联映射对应代谢物组合模型的输出结果作为迭代输出基准;
17、s2-2-2、判断当前时刻t的代谢物数据与基础数据关联映射的代谢物种类是否对应,若是,则执行s2-2-3,否则,放弃处理;
18、s2-2-3、利用当前时刻t的代谢物数据建立迭代起始代谢物组合模型;
19、s2-2-4、利用所述迭代起始代谢物组合模型得到实时代谢物组合模型迭代结果。
20、进一步的,利用所述迭代起始代谢物组合模型得到实时代谢物组合模型迭代结果包括:
21、s2-2-4-1、判断所述迭代起始代谢物组合模型的基础架构与基础数据关联映射对应代谢物组合模型是否一致,若是,则执行s2-2-4-2,否则,返回s2-2-3;
22、s2-2-4-2、获取相邻下一时刻代谢物数据建立迭代循环代谢物组合模型;
23、s2-2-4-3、判断当前迭代循环代谢物组合模型对应代谢物组分是否变化,若是,则输出t时刻至当前时刻的迭代循环代谢物组合模型作为实时代谢物组合模型迭代结果,否则,返回s2-2-4-2;
24、其中,所述变化为代谢物的种类或含量发生变化。
25、进一步的,利用所述实时代谢物组合模型迭代结果基于代谢组学进行复验处理得到数据迭代处理结果包括:
26、s3-1、利用所述实时代谢物组合模型迭代结果进行聚类分析得到实时代谢物组合模型迭代聚类分析结果;
27、s3-2、利用所述实时代谢物组合模型迭代结果获取对应实时代谢物组合模型代谢组学通路数据;
28、s3-3、利用所述实时代谢物组合模型迭代聚类分析结果与实时代谢物组合模型代谢组学通路数据得到数据迭代处理结果。
29、进一步的,利用所述实时代谢物组合模型迭代结果进行聚类分析得到实时代谢物组合模型迭代聚类分析结果包括:
30、s3-1-1、获取所述实时代谢物组合模型迭代结果对应迭代循环代谢物组合模型的产物输出数据作为迭代循环产物输出数据;
31、s3-1-2、利用所述基础数据关联映射作为聚类中心;
32、s3-1-3、利用所述迭代循环产物输出数据与聚类中心基于k-means聚类法得到初始迭代聚类结果;
33、s3-1-4、判断所述实时代谢物组合模型迭代结果对应初始迭代聚类结果与基础数据关联映射是否完全对应,若是,则保留初始迭代聚类结果作为实时代谢物组合模型迭代聚类分析结果,否则,在实时代谢物组合模型迭代结果中删除初始迭代聚类结果对应迭代循环代谢物组合模型,返回s3-1-1。
34、进一步的,利用所述实时代谢物组合模型迭代结果获取对应实时代谢物组合模型代谢组学通路数据包括:
35、利用所述实时代谢物组合模型迭代结果建立实时代谢物组合模型的代谢组学通路图;
36、利用所述代谢组学通路图获取实时代谢物组合模型代谢组学通路特征;
37、利用所述实时代谢物组合模型代谢组学通路特征作为实时代谢物组合模型代谢组学通路数据。
38、进一步的,利用所述代谢组学通路图获取实时代谢物组合模型代谢组学通路特征包括:
39、根据所述代谢组学通路图获取对应酶节点作为代谢组学通路子特征;
40、获取所述代谢组学通路子特征对应代谢物与化合物编号作为代谢组学通路辅助特征;
41、利用所述代谢组学通路子特征与代谢组学通路辅助特征作为实时代谢物组合模型代谢组学通路特征;
42、其中,所述化合物编号基于kegg数据库获取。
43、进一步的,利用所述实时代谢物组合模型迭代聚类分析结果与实时代谢物组合模型代谢组学通路数据得到数据迭代处理结果包括:
44、s3-3-1、判断所述实时代谢物组合模型迭代聚类分析结果中实时代谢物组合模型与实时代谢物组合模型代谢组学通路数据的代谢组学通路子特征是否完全对应,若是,则直接输出实时代谢物组合模型迭代结果作为数据迭代处理结果,否则,执行s3-3-2;
45、s3-3-2、判断所述实时代谢物组合模型迭代聚类分析结果中实时代谢物组合模型对应酶种类的范围是否大于实时代谢物组合模型代谢组学通路数据的代谢组学通路子特征,若是,则输出实时代谢物组合模型中与代谢组学通路子特征对应部分作为数据迭代处理结果,否则,执行s3-3-3;
46、s3-3-3、判断所述实时代谢物组合模型迭代聚类分析结果中实时代谢物组合模型对应酶与实时代谢物组合模型代谢组学通路数据的代谢组学通路辅助特征是否完全对应,若是,则返回s3-1-4,否则,放弃处理。
47、与最接近的现有技术相比,本发明具有的有益效果:
48、在代谢组学及其产物数据的基础上,使用并调整代谢物组合模型的结构与输出,实现了代谢物数据的迭代调整,并引入代谢通路图的酶作为辅助,保证数据快速迭代的同时模型输出的稳定与非离散性。
- 还没有人留言评论。精彩留言会获得点赞!