一种突变NfpAB纳米孔、测试系统及制作方法与应用与流程
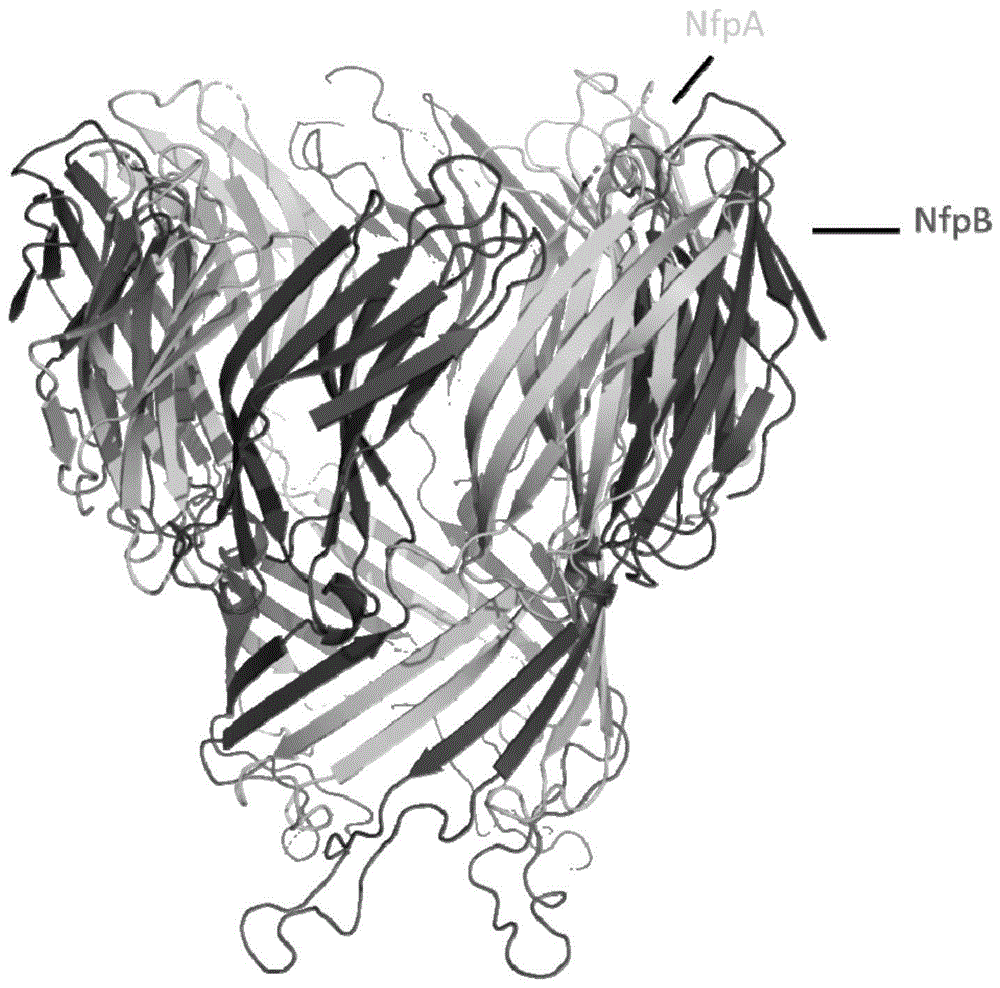
本发明属于纳米孔技术领域,涉及一种新型蛋白纳米孔及其应用,具体地说涉及一种突变nfpab纳米孔、含有该纳米孔的测试系统及其制作方法以及该测试系统在多聚物检测及测序中的应用。
背景技术:
蛋白纳米孔是在生物膜上天然存在的一种由多肽及蛋白复合体组成的跨膜分子通道,其允许离子或大分子通过,从而起到分子运输及信号传导作用,由于这类蛋白通道具有纳米(10-9米)尺度的直径,因此被称为纳米孔。
纳米孔已经成为蛋白检测以及核酸测序的一种强大工具,将纳米孔置于仿生膜上,在膜两端施加一定的电势,离子穿过纳米孔形成的离子流可以用电流值测量。利用这一原理,专利wo2000/28312和stoddartetal.,procnatlacadsci,2009,106,7702-7中描述了一种单通道记录设备的电学检测技术,专利wo2009/077734中则描述了一种多通道的记录技术。
当有分子穿越孔道或与孔道相互作用时,能阻塞孔道从而降低通过的离子流,离子流的降低程度与阻塞孔道的大小或程度正相关,并通过电流值的降低进行测量,利用这一原理,可通过测量电流变化测定分子大小等特征。
纳米孔目前最大应用是在核酸测序领域:将单链或双链核酸穿过纳米孔,测定碱基通过时的电流变化,从而对核酸进行测序。现有的二代高通量核酸测序方法,速度慢且价格昂贵,主要原因是基于光学技术的测量需要通过序列扩增提高信噪比,且需要大量的用于信号检测的专用荧光化学物质。相对于二代测序技术,纳米孔技术不需要进行扩增及荧光标记,极大的节省了时间和成本。
至今,已有a-溶血素、mspa及csgg纳米孔用于核酸测序,研究表明,phi29、clya及frac纳米孔允许双链dna穿过。最近,气单胞菌溶素(aerolysin)被用来区分不同长度的腺嘌呤多聚物。而a-溶血素和clya则可被用于蛋白检测。目前报道的所有这些纳米孔均为由一种单体聚合而成的多聚体。
现有纳米孔道存在着不同程度的技术缺陷,应用于核酸测序领域仍需提高测序准确度。而在蛋白及其他大分子的检测领域,则需要开发合适的孔道进行技术验证及应用开发。因此,亟需开发适用于特定应用的具有更好的空间分辨率和孔道结构的新型纳米孔道。
nfpab是一种来源于皮疽诺卡菌(nocardiafarcinica)的新型纳米孔蛋白,孔道直径约为1.4-1.6nm,是由nfpa及nfpb两种单体蛋白组成的八聚体孔道,孔道内部具有较多的负电荷分布,已有报道将野生型nfpab纳米孔用于测试带正电荷的多肽,但其是否能用于核酸测序、多肽、蛋白检测和测序目前仍然是未知数。
技术实现要素:
为此,本发明正是要解决上述技术问题,从而提出一种突变nfpab纳米孔、含有该纳米孔的测试系统及其制作方法以及该测试系统在多聚物检测及测序中的应用。
为解决上述技术问题,本发明的技术方案为:
本发明提供一种突变nfpab纳米孔,所述纳米孔为由至少一个nfpa蛋白突变单体和至少一个nfpb蛋白突变单体组成的蛋白复合体,或者为由至少两个nfpa与nfpb融合突变基因表达的突变单体组成的蛋白复合体。
作为优选,所述nfpa突变单体由与序列seqidno:1至少70%相同氨基酸序列的多肽组成,所述nfpb突变单体由与序列seqidno:2至少70%相同氨基酸序列的多肽组成。
作为优选,所述突变包括对氨基酸序列任一位点氨基酸的替换、删除、插入中的至少一种。
作为优选,所述nfpa突变单体由序列seqidno:1上1、8、23、49、55、57、67、95、96、107、109、120、125、132、135、145、148、150、169、173中的至少一个位置处的突变得到;所述nfpb突变单体由序列seqidno:2上1、10、17、28、54、60、61、79、84、88、92、96、105、109、124、126、129、130、134、135、153、176、178中的至少一个位置处的突变得到。
作为优选,所述nfpa突变单体包括e55k、e57k、d95r、d96r、d173r突变的至少一种;所述nfpb突变单体包括d17r、e60k、d61r、e88k、d92r、d96r、e105k、e109k、e176k、d178r突变的至少一种。
本发明还提供一种测试系统,其包括所述的突变nfpab纳米孔、膜层和电流测量装置。
作为优选,所述突变nfpab纳米孔设置于第一导电液体介质与第二导电液体介质之间,所述第一导电液体介质与第二导电液体介质中的至少一种中含有分析物。
作为优选,所述突变nfpab纳米孔两端施加有用于控制分析物转位穿过通道和/或限制所述分析物在通道中与孔蛋白相互作用的电场。
作为优选,所述突变nfpab纳米孔嵌入所述膜层中,所述膜层为高分子膜或脂质层。
作为优选,所述脂质层为由磷脂酰胆碱组成的脂质双分子层。
作为优选,所述磷脂酰胆碱为1,2-植烷酰磷脂酰胆碱。
本发明还提供一种制作所述的测试系统的方法,其包括如下步骤:
s1、制备纳米孔蛋白的两种重组表达单体:nfpa蛋白突变体和nfpb蛋白突变体;
s2、将所述表达单体组装为寡聚体;
s3、将寡聚体与膜层相互作用,形成纳米孔。
作为优选,还包括在系统两端施加电场的步骤,所述纳米孔设置于第一导电液体介质和第二导电液体介质之间,至少一种导电液体介质中含有分析物。
作为优选,还包括通过测量离子电流鉴定分析物和/或检测分析物浓度的步骤。
作为优选,所述分析物为核苷酸、核酸、氨基酸、寡聚肽、多肽、蛋白质、多聚物、药物、离子、污染物、纳米级物质中的一种。
作为优选,所述核酸为单链dna、双链dna、rna中的至少一种。
本发明还提供一种所述的测试系统在生物多聚体检测或测序中的应用。
作为优选,所述生物多聚体为核酸、多肽或蛋白中的一种。
作为优选,所述核酸为单链dna、双链dna、rna中的至少一种。
作为优选,采用所述测试系统进行多聚体检测或测序包括如下步骤:
a、组建含nfpab突变纳米孔及膜层的测试系统;
b、施加电压,使多聚物与所述纳米孔接触,并使所述多聚物相对于所述纳米孔移动;
c、在所述多聚物相对于所述纳米孔移动时,获取至少一个电流值,所述电流值指示所述多聚物的至少一个特征,表征所述多聚物。
作为优选,所述特征包括多聚物的长度、特性、序列、二级结构以及是否具有修饰中的至少一种。
本发明的上述技术方案相比现有技术具有以下优点:
(1)本发明提供了一种突变nfpab纳米孔,所述纳米孔为由至少一个nfpa蛋白突变单体和至少一个nfpb蛋白突变单体组成的蛋白复合体,或者为由至少两个nfpa与nfpb融合突变基因表达的突变单体组成的蛋白复合体。所述突变nfpab纳米孔是一种新型突变纳米孔,具有与现有技术中已知纳米孔不同的结构和识别位点,提高了测序的准确度、降低了错误率。所述nfpab突变体允许捕捉及转移单链dna(ssdna)并区分腺嘌呤(a),胸腺嘧啶(t),胞嘧啶(c)及鸟嘌呤(g)。另外,所述nfpab突变体具有类似于mspa的锥形孔道结构,是核酸测序的理想孔道。
(2)本发明所述的测试系统,包括所述突变nfpab纳米孔、膜层和电流测量装置,电场力和电渗流是驱动核酸分子进入孔道中的主要驱动力。通过对纳米孔内部的工程化定点突变,调整孔道内部的电荷分布,从而降低核酸穿过孔道时的速度,使碱基的精准识别成为可能。
(3)本发明所述的测试系统,所述突变nfpab纳米孔两端施加有用于控制分析物转位穿过通道和/或限制所述分析物在通道中与孔蛋白相互作用的电场。该系统可满足两种不同情况的测试,一种情况下,这一系统能控制分析物转运穿过孔道。另一种情况下,这一系统置于特定电场中,使分析物与纳米孔相互作用从而检测分析物的一种特征。施加的电势(用以产生电场)得以产生电流。电流值作为输出信号。例如,这一系统包含将纳米孔至于特定电场中,使分析物进行在电泳或电渗作用下穿过和/或捕获在纳米孔中,从而检测分析物的某种特征。这一特征可以是分析物的电学特征,化学特征或物理特征。
(4)本发明所述的测试系统,所述突变nfpab纳米孔嵌入所述膜层中,所述膜层为高分子膜或脂质层。将纳米孔嵌入到膜层中,对nfpab纳米孔进行了工程化改造,以允许dna电泳时被捕获并能区分不同碱基信号。与其他用于dna测序的纳米孔不同(如a-溶血素、mspa及csgg),nfpab由两种不同的单体组成,这使得对其工程化改造能分别对nfpa及nfpb进行定点突变,对不同突变体进行组合从而增加了改造的灵活度,提高了改造空间。与其他纳米孔由均一单体构成纳米孔的全对称的结构不同,nfpab由nfpa及nfpb交叉分布组成,使得分子在其内部可以具有一定的方向性,这为分析物的鉴定提供了另一个空间维度。此外,nfpab类似于mspa的锥形结构,能更加精准的区分单个碱基。所述系统中,nfpa及nfpb工程化表达蛋白可能在其c端融合了一个蛋白标签,如组氨酸(his)标签或麦芽糖标签(mbp),便于蛋白的提取纯化。
附图说明
为了使本发明的内容更容易被清楚的理解,下面根据本发明的具体实施例并结合附图,对本发明作进一步详细的说明,其中
图1是本发明实施例所述的突变nfpab纳米孔的结构模型;
图2是本发明实施例所述的突变nfpab纳米孔氨基酸电荷分布俯视图;
图3是本发明实施例所述的突变nfpab纳米孔中nfpa突变单体蛋白表达条件优化图;
图4是本发明实施例所述的突变nfpab纳米孔中nfpb突变单体蛋白表达条件优化图;
图5是nfpa及nfpb突变单体蛋白表达溶解性图;
图6是nfpa及nfpb突变单体蛋白二聚体图;
图7是聚核苷酸poly(dt)70在野生型nfpab纳米孔中电流轨迹和典型事件图;
图8是聚核苷酸poly(dt)70通过纳米孔突变体nfpab-m1电流轨迹和典型事件图;
图9是聚核苷酸poly(da)70通过纳米孔突变体nfpab-m1电流轨迹和典型事件图;
图10是聚核苷酸poly(dc)70通过纳米孔突变体nfpab-m1电流轨迹和典型事件图;
图11是已知单链核酸ssdna1(seqidno:3)通过纳米孔突变体nfpab-m1电流轨迹和典型事件图;
图12是已知单链核酸ssdna1(seqidno:3)通过纳米孔突变体nfpab-m2电流轨迹和典型事件图;
图13是多肽poly(r)7通过纳米孔突变体nfpab-m1电流轨迹和典型事件图。
具体实施方式
实施例1
本实施例提供一种突变nfpab纳米孔,如图1所示,所述纳米孔为由至少一个nfpa蛋白突变体和至少一个nfpb蛋白突变体组成的蛋白复合体,或者为由至少两个nfpa与nfpb融合突变基因表达的突变单体组成的蛋白复合体。所述纳米孔的电荷分布如图2所示。
(1)首先构建nfpa和nfpb野生型载体:
从ncbi网站获得野生型nfpa序列(编号:nfa15890)及nfpb序列(编号:nfa15900),所述nfpa突变单体由与序列seqidno:1至少70%相同氨基酸序列的多肽组成,所述nfpb突变单体由与序列seqidno:2至少70%相同氨基酸序列的多肽组成。其中,野生型nfpa的单体蛋白序列(seqidno:1)为:
dtfvplpdgqkvgpgvtitrtgehavispsmaangagrvawvsgnatadvtvtpegevgpnngpagdpgtnnssthgasqlntgyivgcqvsigddaisaglsggidleggsiggsigldlgpgdvkfvqidykditkpgvysveyqdveiqiqgcagyaqarsytvveiigdhyskttlygmpfsig。
野生型nfpb的单体蛋白序列(seqidno:2)为:
dtfvplpggeitktlsdgtvvtvrlvgesatispsmgatpvhrnawvsgsaqveisgggedvggkiypgyvvgcqvnidgggveggvegsadwsgdtvtggvgaesggeltlgpgqaksfyildiekpddygnedhatnnkfkgnsgsvtwadstiglsgcagyaqarsfvkvkvetdnvmsvvtlwgqpfslg。
对两序列进行基于大肠杆菌表达的密码子优化,使密码子偏好性符合大肠杆菌工程化表达。并在片段上游加上ecori酶切位点(gaattc),下游加上xhoi酶切位点(ctcgag),构建的dna序列nfpa-wt如序列表seqidno:4所示,nfpb-wt如序列表seqidno:5所示,人工合成两序列。
大肠杆菌密码子优化的野生型nfpa的dna序列(seqidno:4)为:
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttaccattacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggtcgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccggaaggcgaagttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacggcgcaagccagctgaataccggttatattgtcggctgccaggttagtattggcgacgacgcaattagcgcaggtctgtctggcggtattgatctggaaggcggtagcattggcggtagtattggtctggatctgggtccgggggacgttaaatttgttcagatcgactacaaagacatcaccaaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggttgcgcaggttacgcacaggcacgcagctataccgttgtcgaaattatcggggatcactatagcaaaaccaccctgtacggtatgccgtttagtatcggtctcgag。
大肠杆菌密码子优化的野生型nfpb的dna序列(seqidno:5)为:
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctgacggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatgggcgcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttccggcggcggtgaagacgttggcggcaaaatttatccgggttatgtggtcggctgccaggttaacattgacggtggtggcgtagaaggcggcgttgaaggttctgcagattggtctggcgataccgttaccggtggtgtaggcgcagaatctggcggcgaactgaccctgggtccgggtcaagcaaaaagcttctacatcctggacatcgagaaaccggacgattacggtaacgaagatcacgcgaccaacaacaaattcaaaggcaacagcggcagcgtcacctgggcagatagtaccattggcctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaaagtcaaagtcgagaccgacaacgtcatgtctgttgttacgctgtggggtcaaccgtttagtctgggtctcgag。
将上述合成的nfpa-wt及nfpb-wt基因及载体pet21a质粒分别用ecori和xhoi内切酶(neb)在37℃下进行双酶切2h,将酶切的基因片段用1%琼脂糖凝胶电泳分离,切胶回收目的片段。用t4dna连接酶将回收的nfpa-wt及nfpb-wt片段分别与回收的pet21a片段在16℃下进行过夜连接。将构建好的载体转化大肠杆菌dh5α感受态细胞,42℃热击90s,冰上静置2min,加入1mllb培养基在37℃下预培养1h,菌液离心后涂布于lb抗性(含100μg/ml氨苄青霉素)平板,在37℃培养过夜。用菌落pcr对lb平板(含100μg/ml氨苄青霉素)上的单菌落进行阳性克隆验证。阳性单菌落转5mllb中(含100μg/ml氨苄青霉素)培养后进行基因测序验证序列。
(2)载体的突变和转化
取构建好的野生型基因载体pet21a-nfpa-wt,用多点突变试剂盒(takara)对e55,e57,d95,d96,d173位点进行定点突变为k55,k57,r95,r96,r173,对pet21a-nfpb-wt进行d17,e60,d61,e88,d92,d96,e105,e109,e176,d178位点进行定点突变为r17,k60,r61,k88,r92,r96,k105,k109,k176,r178。分别获得的阳性菌落扩大培养后提取质粒,分别进行基因测序验证及双酶切验证,获得突变质粒pet21a-nfpa-m1及pet21a-nfpb-m1,突变序列分别如序列表seqidno:6及seqidno:7所示。
突变体nfpab-m1的nfpa突变单体dna序列(seqidno:6)为:
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttaccattacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggtcgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccgaaaggcaaagttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacggcgcaagccagctgaataccggttatattgtcggctgccaggttagtattggccgccgcgcaattagcgcaggtctgtctggcggtattgatctggaaggcggtagcattggcggtagtattggtctggatctgggtccgggggacgttaaatttgttcagatcgactacaaagacatcaccaaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggttgcgcaggttacgcacaggcacgcagctataccgttgtcgaaattatcgggcgccactatagcaaaaccaccctgtacggtatgccgtttagtatcggtctcgag。
突变体nfpab-m1的nfpb突变单体dna序列(seqidno:7)为:
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctcgtggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatgggcgcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttccggcggcggtaaacgtgttggcggcaaaatttatccgggttatgtggtcggctgccaggttaacattgacggtggtggcgtagaaggcggcgttaaaggttctgcacgttggtctggccgtaccgttaccggtggtgtaggcgcaaaatctggcggcaaactgaccctgggtccgggtcaagcaaaaagcttctacatcctggacatcgagaaaccggacgattacggtaacgaagatcacgcgaccaacaacaaattcaaaggcaacagcggcagcgtcacctgggcagatagtaccattggcctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaaagtcaaagtcaaaacccgtaacgtcatgtctgttgttacgctgtggggtcaaccgtttagtctgggtctcgag。
(3)突变单体蛋白的表达与纯化
a、转化
取1μl突变质粒pet21a-nfpa-m1及pet21a-nfpb-m1分别转化大肠杆菌表达菌株bl21(de3)感受态,42℃热击90s,冰上静置2min,加入1mllb培养基37℃预培养1h,菌液离心后涂布lb抗性(含100μg/ml氨苄青霉素)平板,37℃培养过夜。
b、表达条件优化
挑取平板上转化的阳性单菌落,接入3mllb培养基(含100μg/ml氨苄青霉素)中,在37℃、200rpm下过夜培养。取菌液按1:100接入50mllb培养基(含100μg/ml氨苄青霉素)中,在37℃、200rpm下培养3h左右,od600值达到0.5-0.7时,加入终浓度为0.5mm的iptg诱导nfpa-m1及nfpb-m1蛋白表达,在30℃、200rpm下培养。分别于0h(添加iptg前),2h、4h、6h、8h、on(过夜诱导)取2ml菌液于离心管中,5000rpm离心3min收集菌体,弃上清,菌体沉淀-80℃保存待用。过夜诱导的剩余菌液约38ml置于50ml离心管中5000rpm离心3min收集菌体,弃上清,菌体沉淀-80℃保存待用。
取不同时间点保存菌体加入200μlsds上样缓冲液(200mmtris-hcl(ph6.8),8%sds(m/v),0.4%溴酚蓝(m/v),40%甘油(v/v),400mmβ-巯基乙醇使用前加入),95℃下处理10min。4℃、12000rpm下离心20min,上清即为全蛋白(tp)。将各样品全蛋白用改良型bca试剂盒(生工)测量蛋白浓度。
sds-page检测:准备12%的sds-page胶,分别取nfpa-m1及nfpb-m1于0h(添加iptg前),2h,4h,6h,8h,on(过夜诱导)的全蛋白样品各50μg上样,80v电泳20min,120v电泳60min。凝胶用考马斯亮蓝染色液(10%乙酸,45%甲醇,45%水,0.25%(m/v)考马斯亮蓝r-250)染色30min,其后用脱色液(10%乙酸,45%甲醇,45%水)脱色3次,至蛋白条带清晰可见。结果显示,nfpa-m1及nfpb-m1均表达成功(参见图3与图4)。
c、单体蛋白表达溶解性
取过夜诱导表达的菌液菌体38ml,分别提取可溶性蛋白及包涵体蛋白鉴定蛋白表达溶解性。菌体用5mlpbs溶菌缓冲液(137mmnacl,2.7mmkcl,10mmna2hpo4,2mmkh2po4,ph7.4使用前加入0.2mg/ml溶菌酶,20μg/mldnasei,1mmmgcl2,1mmpmsf)悬浮,冰上孵育30min。超声破碎10min,功率100w,4s超声4s暂停,全程在冰上操作。12000rpm下离心30min,收集上清液即为可溶性蛋白(sp)。沉淀加入5ml包涵体溶解缓冲液(20mmtris-hcl,500mmnacl,8m尿素,5mm咪唑,ph8.0)悬浮,室温下孵育1h。12000rpm离心30min,上清为包涵体蛋白(ib)。
sds-page检测:分别取nfpa及nfpb各50μg全蛋白(tp),可溶性蛋白(sp),包涵体蛋白(ib)用12%sds-page进行凝胶电泳分离,80v电泳20min,随后120v电泳60min。凝胶用考马斯亮蓝染色液染色30min,脱色三次。结果如图5所示,nfpa及nfpb单体均在包涵体中表达。
d、大量诱导表达
将50ml培养瓶中过夜活化培养的菌液按1:100接种于1l的lb液体培养基(含100μg/ml氨苄青霉素)中,在37℃、200rpm下培养3h左右,使od600值达到0.5-0.7时,加入终浓度为0.5mm的iptg诱导蛋白表达,在30℃、200rpm下培养4h,离心收集细胞菌体,pbs洗涤一次,弃上清,菌体沉淀-80℃保存待用。
e、单体蛋白纯化
包涵体蛋白提取:将收集的细菌菌体加入20mlpbs溶菌缓冲液(内含0.2mg/ml溶菌酶,20μg/mldnasei,1mmmgcl2,1mmpmsf),冰上孵育30min。超声破碎10min,超声功率为100w,4s超声,4s暂停,全程在冰上操作。在12000rpm下离心30min,弃上清,沉淀加入5ml结合/清洗缓冲液(20mmtris-hcl,500mmnacl,8m尿素,5mm咪唑,ph8.0)悬浮,室温下孵育1h。12000rpm离心30min,上清为包涵体蛋白(ib),其中包含单体蛋白。
ni-nta亲和层析纯化:取4mlni-nta琼脂糖纯化树脂,填充到层析柱中,确保没有气泡,用5倍柱床体积的结合/清洗缓冲液对树脂进行平衡。
将包涵体蛋白用0.45μm的过滤器过滤,将过滤后的全蛋白上样至柱子,收集流穿液到离心管中,将流穿液再次上样,重新流通一次,提高蛋白结合率。
用两倍柱床体积的结合/清洗缓冲液清洗柱子,重复这一步骤,直至流穿液的od280接近基线。
用两倍柱床体积的洗脱缓冲液(20mmtris-hcl,500mmnacl,8m尿素,500mm咪唑,ph8.0)洗脱柱上的nfpa-m1及nfpb-m1标签蛋白。重复两次,每次的洗脱液分别保存。
超滤纯化:将亲和层析获得的洗脱液用10kda超滤管(millipore)进行超滤浓缩,去除杂蛋白,同时用结合/清洗缓冲液替换洗脱缓冲液。
(4)蛋白单体的复性与聚合
用改良型bca试剂盒分别对纯化好的nfpa-m1及nfpb-m1单体蛋白进行浓度检测。取nfpa-m1及nfpb-m1单体蛋白按1:1质量比(各20μg)混合,加入去离子水至400μl,再加入600μl饱和硫酸钠溶液,4℃过夜沉淀。其后,4℃,18000g离心30min,弃净上清。沉淀蛋白用50μl的溶解缓冲液(10mmtris-cl,150mmnacl,1%tritonx-100)过夜孵育,使蛋白复性折叠并聚合成二聚体,nfpa及nfpb单体及二聚体如图6所示。
本实施例还提供一种含上述突变nfpab纳米孔的测试系统,所述测试系统还包括膜层和电流测量装置。其中,突变nfpab纳米孔设置于第一导电液体介质与第二导电液体介质之间,所述第一导电液体介质与第二导电液体介质中的至少一种中含有分析物。所述突变nfpab纳米孔两端施加有电场。所述膜层优选为由磷脂酰胆碱组成的脂质双分子层,所述磷脂酰胆碱为1,2-植烷酰磷脂酰胆碱。
本实施例还提供一种利用上述测试系统检测单链dna(ssdna)的方法,其包括如下步骤:
1、制备试剂
(1)溶液a:1mkcl,10mmtris-hcl,1mmedta,ph7.5。
(2)100nmssdna溶液:将1nmolssdna溶解于10ml溶液a中,即得。
(3)1mg/mlnfpab-m1蛋白突变体溶液:将1mgnfpab-m1蛋白突变体溶解于1ml溶液a中,即得。
(4)10mg/mldphpc正癸烷溶液:将10mgdphpc溶解于1ml正癸烷中,即得。
(5)测试液:将1μl上述所配制的nfpab-m1蛋白突变体溶液加入至99μl上述所配制的ssdna溶液中,充分混匀。
2、制备磷脂双分子层
磷脂双分子层膜的构建采用喷涂的方法,具体操作为:将测试液加入至已洗净的测试流体池的内外部,此时流体池中的测试液通过内外部之间隔绝层上的100μm小孔为连续状态。用10μl移液枪头沾取dphpc正癸烷溶液,并伸入至流体池外部的测试液中,对准隔绝层上的100μm小孔通过移液枪吹入空气,使形成的气泡与隔绝层接触,此时,dphpc分子会自发在100μm小孔处形成双分子层膜。在流体池内外部加100mv电压,可观察到电流从无磷脂膜时的过载变为0。
3、突变体nfpab-m1纳米孔单通道组装
测试液中的nfpab蛋白突变体可自发在磷脂双分子层上组装形成纳米孔单通道,形成纳米孔嵌于膜层的结构。
4、数据采集
通过信号采集设备(如moleculardevices公司的axopatch200b或其他可用于微小电流检测的数据采集设备)在流体池内外部施加-100mv电压,自动化检索ssdna穿孔事件,并记录该事件的电流振幅和持续时间。通过测量离子电流可鉴定分析物和检测分析物浓度,其中鉴定分析物是指当分析物与纳米孔相互作用时测量离子电流以获得电流模式来检测分析物,其中电流模式中阻塞电流的出现显示分析物的存在。对于未知分析物,将未知分析物测量获得的电流模式与在相同条件下使用已知的分析物测量获得的电流模式进行比较,从而鉴定分析物。对于浓度分析,通过将单位时间内未知分析物的检出频次与在相同条件下已知浓度的分析物的检出频次进行比较,从而获得分析物浓度。
5、数据分析
通过归一化的电流-时间曲线可观察到nfpab-m1蛋白突变体在dphpc中形成稳定的单通道并存在长时间稳定的开孔电流,同时能观察到大量ssdna穿孔事件信号(如图8-10所示),所述聚核苷酸poly(dt)70在野生型nfpab纳米孔中电流轨迹和典型事件如图7所示,野生型nfpab孔道内部负电荷较多,可以观测到nfpab蛋白嵌膜,poly(dt)70无法穿孔。通过对ssdna堵孔电流的时序分析,可以得到ssdna内部序列的信息。
实施例2
本实施例提供一种突变nfpab纳米孔和含有该纳米孔的测试系统,其与对比文件1基本相同,不同之处在于,利用所得蛋白突变体nfpab-m1进行已知单链核酸ssdna1(seqidno:3)检测,检测结果如图11所示。所述单链核酸ssdna1的基因序列(seqidno:3)为:
atccggatatagttcctcctttcagcaaaaaacccctcaagacccgtttagaggccccaaggggttatgctagttattgctcagcggtggcagcagccaactcagcttcctttcgggctttgttagcagccggatctcagtggtggtggtggtggtgctcgagtgcggccgcaagcttgtcgacggagctcgaattcggatccgcgacccatttgctgtccaccagtcatgctagccatatgtatatctccttcttaaagttaaacaaaattatttctagaggggaattgttatccgctcacaattcccctatagtgagtcgtattaatttcgcgggatcgagatctcgatcctctacgccggacgcatcgtggccggcatcaccggcgccacaggtgcggttgctggcgcctatatcgccgacatcaccgatggggaagatcgggctcgccacttcgggctcatgagcgcttgtttcggcgtgggtatggtggcaggccccgtggccgggggactgttgggcgccatctccttgcatgcaccattccttgcggcggcggtgctcaacggcctcaacctactactgggctgcttcctaatgcaggagtcgcataagggagagcgtcgagatcccggacaccatcgaatggcgcaaaacctttcgcggtatggcatgatagcgcccggaagagagtcaattcagggtggtgaatgtgaaaccagtaacgttatacgatgtcgcagagtatgccggtgtctcttatcagaccgtttcccgcgtggtgaaccaggccagccacgtttctgcgaaaacgcgggaaaaagtggaagcggcgatggcggagctgaattacattcccaaccgcgtggcacaacaactggcgggcaaacagtcgttgctgattggcgttgccacctccagtctggccctgcacgcgccgtcgcaaattgtcgcggcgattaaatctcgcgccgatcaactgggtgccagcgtggtggtgtcgatggtagaacgaagcggcgtcgaagcctgtaaagcggcggtgcacaatcttctcgcgcaacgcgtcagtgggctgatcattaactatccgctggatgaccaggatgccattgctgtggaagctgcctgcactaatgttccggcgttatttcttgatgtctctgaccagacacccatcaacagtattattttctcccatgaagacggtacgcgactgggcgtggagcatctggtcgcattgggtcaccagcaaatcgcgctgttagcgggcccattaagttctgtctcggcgcgtctgcgtctggctggctggcataaatatctcactcgcaatcaaattcagccgatagcggaacgggaaggcgactggagtgccatgtccggttttcaacaaaccatgcaaatgctgaatgagggcatcgttcccactgcgatgctggttgccaacgatcagatggcgctgggcgcaatgcgcgccattaccgagtccgggctgcgcgttggtgcggatatctcggtagtgggatacgacgataccgaagacagctcatgttatatcccgccgttaaccaccatcaaacaggattttcgcctgctggggcaaaccagcgtggaccgcttgctgcaactctctcagggccaggcggtgaagggcaatcagctgttgcccgtctcactggtgaaaagaaaaaccaccctggcgcccaatacgcaaaccgcctctccccgcgcgttggccgattcattaatgcagctggcacgacaggtttcccgactggaaagcgggcagtgagcgcaacgcaattaatgtaagttagctcactcattaggcaccgggatctcgaccgatgcccttgagagccttcaacccagtcagctccttccggtgggcgcggggcatgactatcgtcgccgcacttatgactgtcttctttatcatgcaactcgtaggacaggtgccggcagcgctctgggtcattttcggcgaggaccgctttcgctggagcgcgacgatgatcggcctgtcgcttgcggtattcggaatcttgcacgccctcgctcaagccttcgtcactggtcccgccaccaaacgtttcggcgagaagcaggccattatcgccggcatggcggccccacgggtgcgcatgatcgtgctcctgtcgttgaggacccggctaggctggcggggttgccttactggttagcagaatgaatcaccgatacgcgagcgaacgtgaagcgactgctgctgcaaaacgtctgcgacctgagcaacaacatgaatggtcttcggtttccgtgtttcgtaaagtctggaaacgcggaagtcagcgccctgcaccattatgttccggatctgcatcgcaggatgctgctggctaccctgtggaacacctacatctgtattaacgaagcgctggcattgaccctgagtgatttttctctggtcccgccgcatccataccgccagttgtttaccctcacaacgttccagtaaccgggcatgttcatcatcagtaacccgtatcgtgagcatcctctctcgtttcatcggtatcattacccccatgaacagaaatcccccttacacggaggcatcagtgaccaaacaggaaaaaaccgcccttaacatggcccgctttatcagaagccagacattaacgcttctggagaaactcaacgagctggacgcggatgaacaggcagacatctgtgaatcgcttcacgaccacgctgatgagctttaccgcagctgcctcgcgcgtttcggtgatgacggtgaaaacctctgacacatgcagctcccggagacggtcacagcttgtctgtaagcggatgccgggagcagacaagcccgtcagggcgcgtcagcgggtgttggcgggtgtcggggcgcagccatgacccagtcacgtagcgatagcggagtgtatactggcttaactatgcggcatcagagcagattgtactgagagtgcaccatatatgcggtgtgaaataccgcacagatgcgtaaggagaaaataccgcatcaggcgctcttccgcttcctcgctcactgactcgctgcgctcggtcgttcggctgcggcgagcggtatcagctcactcaaaggcggtaatacggttatccacagaatcaggggataacgcaggaaagaacatgtgagcaaaaggccagcaaaaggccaggaaccgtaaaaaggccgcgttgctggcgtttttccataggctccgcccccctgacgagcatcacaaaaatcgacgctcaagtcagaggtggcgaaacccgacaggactataaagataccaggcgtttccccctggaagctccctcgtgcgctctcctgttccgaccctgccgcttaccggatacctgtccgcctttctcccttcgggaagcgtggcgctttctcatagctcacgctgtaggtatctcagttcggtgtaggtcgttcgctccaagctgggctgtgtgcacgaaccccccgttcagcccgaccgctgcgccttatccggtaactatcgtcttgagtccaacccggtaagacacgacttatcgccactggcagcagccactggtaacaggattagcagagcgaggtatgtaggcggtgctacagagttcttgaagtggtggcctaactacggctacactagaaggacagtatttggtatctgcgctctgctgaagccagttaccttcggaaaaagagttggtagctcttgatccggcaaacaaaccaccgctggtagcggtggtttttttgtttgcaagcagcagattacgcgcagaaaaaaaggatctcaagaagatcctttgatcttttctacggggtctgacgctcagtggaacgaaaactcacgttaagggattttggtcatgagattatcaaaaaggatcttcacctagatccttttaaattaaaaatgaagttttaaatcaatctaaagtatatatgagtaaacttggtctgacagttaccaatgcttaatcagtgaggcacctatctcagcgatctgtctatttcgttcatccatagttgcctgactccccgtcgtgtagataactacgatacgggagggcttaccatctggccccagtgctgcaatgataccgcgagacccacgctcaccggctccagatttatcagcaataaaccagccagccggaagggccgagcgcagaagtggtcctgcaactttatccgcctccatccagtctattaattgttgccgggaagctagagtaagtagttcgccagttaatagtttgcgcaacgttgttgccattgctgcaggcatcgtggtgtcacgctcgtcgtttggtatggcttcattcagctccggttcccaacgatcaaggcgagttacatgatcccccatgttgtgcaaaaaagcggttagctccttcggtcctccgatcgttgtcagaagtaagttggccgcagtgttatcactcatggttatggcagcactgcataattctcttactgtcatgccatccgtaagatgcttttctgtgactggtgagtactcaaccaagtcattctgagaatagtgtatgcggcgaccgagttgctcttgcccggcgtcaatacgggataataccgcgccacatagcagaactttaaaagtgctcatcattggaaaacgttcttcggggcgaaaactctcaaggatcttaccgctgttgagatccagttcgatgtaacccactcgtgcacccaactgatcttcagcatcttttactttcaccagcgtttctgggtgagcaaaaacaggaaggcaaaatgccgcaaaaaagggaataagggcgacacggaaatgttgaatactcatactcttcctttttcaatattattgaagcatttatcagggttattgtctcatgagcggatacatatttgaatgtatttagaaaaataaacaaataggggttccgcgcacatttccccgaaaagtgccacctgaaattgtaaacgttaatattttgttaaaattcgcgttaaatttttgttaaatcagctcattttttaaccaataggccgaaatcggcaaaatcccttataaatcaaaagaatagaccgagatagggttgagtgttgttccagtttggaacaagagtccactattaaagaacgtggactccaacgtcaaagggcgaaaaaccgtctatcagggcgatggcccactacgtgaaccatcaccctaatcaagttttttggggtcgaggtgccgtaaagcactaaatcggaaccctaaagggagcccccgatttagagcttgacggggaaagccggcgaacgtggcgagaaaggaagggaagaaagcgaaaggagcgggcgctagggcgctggcaagtgtagcggtcacgctgcgcgtaaccaccacacccgccgcgcttaatgcgccgctacagggcgcgtcccattcgcca。
实施例3
本实施例提供一种突变nfpab纳米孔及含有该纳米孔的测试系统,其与实施例1基本相同,不同之处在于,采用包含nfpa-m2(seqidno:8)及nfpb-m2(seqidno:9)核苷酸序列的基因,最后制得包含nfpa-m2(seqidno:10)及nfpb-m2(seqidno:11)所示氨基酸序列的nfpab-m2。利用所得nfpab-m2进行已知单链核酸ssdna1(seqidno:3)检测,其增加了孔道内部的正电荷数量,一定程度上降低了单链dna过孔速率,增加检测精度。测试结果如图12所示。
其中突变体nfpab-m2的nfpa突变单体dna序列(seqidno:8)为:
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttaccattacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggtcgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccgaaaggcaaagttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacggcgcaagccagctgaataccggttatattgtcggctgccaggttagtattggccgccgcgcaattagcgcaggtctgtctggcggtattcgcctgaaaggcggtagcattggcggtagtattggtctgcgcctgggtccgggggacgttaaatttgttcagatcgactacaaagacatcaccaaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggttgcgcaggttacgcacaggcacgcagctataccgttgtcgaaattatcgggcgccactatagcaaaaccaccctgtacggtatgccgtttagtatcggtctcgag。
突变体nfpab-m2的nfpb突变单体dna序列(seqidno:9)为:
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctcgtggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatgggcgcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttccggcggcggtaaacgtgttggcggcaaaatttatccgggttatgtggtcggctgccaggttaacattcgtggtggtggcgtaaaaggcggcgttaaaggttctgcacgttggtctggccgtaccgttaccggtggtgtaggcgcaaaatctggcggcaaactgaccctgggtccgggtcaagcaaaaagcttctacatcctgcgtatcaaaaaaccgcgtcgttacggtaacgaagatcacgcgaccaacaacaaattcaaaggcaacagcggcagcgtcacctgggcagatagtaccattggcctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaaagtcaaagtcaaaacccgtaacgtcatgtctgttgttacgctgtggggtcaaccgtttagtctgggtctcgag。
突变体nfpab-m2的nfpa突变单体蛋白序列(seqidno:10)为:
dtfvplpdgqkvgpgvtitrtgehavispsmaangagrvawvsgnatadvtvtpegevgpnngpagdpgtnnssthgasqlntgyivgcqvsignnaisaglsggidleggsiggsigldlgpgdvkfvqidykditkpgvysveyqdveiqiqgcagyaqarsytvveiigdhyskttlygmpfsig。
突变体nfpab-m2的nfpb突变单体蛋白序列(seqidno:11)为:
dtfvplpggeitktlsdgtvvtvrlvgesatispsmgatpvhrnawvsgsaqveisgggedvggkiypgyvvgcqvnidgggveggvqgsanwsgntvtggvgaqsggqltlgpgqaksfyildiekpddygnedhatnnkfkgnsgsvtwadstiglsgcagyaqarsfvkvkvetdnvmsvvtlwgqpfslg。
实施例4
本实施例提供一种突变nfpab纳米孔及含有该纳米孔的测试系统,其与实施例1基本相同,不同之处在于,利用所得蛋白nfpab-m1突变体进行多肽(poly(r)7)检测,检测结果如图13所示。
显然,上述实施例仅仅是为清楚地说明所作的举例,而并非对实施方式的限定。对于所属领域的普通技术人员来说,在上述说明的基础上还可以做出其它不同形式的变化或变动。这里无需也无法对所有的实施方式予以穷举。而由此所引伸出的显而易见的变化或变动仍处于本发明创造的保护范围之中。
序列表
<110>深圳市梅丽纳米孔科技有限公司
<120>一种突变nfpab纳米孔、测试系统及制作方法与应用
<130>jy191-0292
<160>11
<170>siposequencelisting1.0
<210>1
<211>188
<212>prt
<213>artificial
<400>1
aspthrphevalproleuproaspglyglnlysvalglyproglyval
151015
thrilethrargthrglygluhisalavalileserprosermetala
202530
alaasnglyalaglyargvalalatrpvalserglyasnalathrala
354045
aspvalthrvalthrprogluglygluvalglyproasnasnglypro
505560
alaglyaspproglythrasnasnserserthrhisglyalasergln
65707580
leuasnthrglytyrilevalglycysglnvalserileglyaspasp
859095
alaileseralaglyleuserglyglyileaspleugluglyglyser
100105110
ileglyglyserileglyleuaspleuglyproglyaspvallysphe
115120125
valglnileasptyrlysaspilethrlysproglyvaltyrserval
130135140
glutyrglnaspvalgluileglnileglnglycysalaglytyrala
145150155160
glnalaargsertyrthrvalvalgluileileglyasphistyrser
165170175
lysthrthrleutyrglymetpropheserilegly
180185
<210>2
<211>194
<212>prt
<213>artificial
<400>2
aspthrphevalproleuproglyglygluilethrlysthrleuser
151015
aspglythrvalvalthrvalargleuvalglygluseralathrile
202530
serprosermetglyalathrprovalhisargasnalatrpvalser
354045
glyseralaglnvalgluileserglyglyglygluaspvalglygly
505560
lysiletyrproglytyrvalvalglycysglnvalasnileaspgly
65707580
glyglyvalgluglyglyvalgluglyseralaasptrpserglyasp
859095
thrvalthrglyglyvalglyalagluserglyglygluleuthrleu
100105110
glyproglyglnalalysserphetyrileleuaspileglulyspro
115120125
aspasptyrglyasngluasphisalathrasnasnlysphelysgly
130135140
asnserglyservalthrtrpalaaspserthrileglyleusergly
145150155160
cysalaglytyralaglnalaargserphevallysvallysvalglu
165170175
thraspasnvalmetservalvalthrleutrpglyglnpropheser
180185190
leugly
<210>3
<211>5443
<212>dna
<213>artificial
<400>3
atccggatatagttcctcctttcagcaaaaaacccctcaagacccgtttagaggccccaa60
ggggttatgctagttattgctcagcggtggcagcagccaactcagcttcctttcgggctt120
tgttagcagccggatctcagtggtggtggtggtggtgctcgagtgcggccgcaagcttgt180
cgacggagctcgaattcggatccgcgacccatttgctgtccaccagtcatgctagccata240
tgtatatctccttcttaaagttaaacaaaattatttctagaggggaattgttatccgctc300
acaattcccctatagtgagtcgtattaatttcgcgggatcgagatctcgatcctctacgc360
cggacgcatcgtggccggcatcaccggcgccacaggtgcggttgctggcgcctatatcgc420
cgacatcaccgatggggaagatcgggctcgccacttcgggctcatgagcgcttgtttcgg480
cgtgggtatggtggcaggccccgtggccgggggactgttgggcgccatctccttgcatgc540
accattccttgcggcggcggtgctcaacggcctcaacctactactgggctgcttcctaat600
gcaggagtcgcataagggagagcgtcgagatcccggacaccatcgaatggcgcaaaacct660
ttcgcggtatggcatgatagcgcccggaagagagtcaattcagggtggtgaatgtgaaac720
cagtaacgttatacgatgtcgcagagtatgccggtgtctcttatcagaccgtttcccgcg780
tggtgaaccaggccagccacgtttctgcgaaaacgcgggaaaaagtggaagcggcgatgg840
cggagctgaattacattcccaaccgcgtggcacaacaactggcgggcaaacagtcgttgc900
tgattggcgttgccacctccagtctggccctgcacgcgccgtcgcaaattgtcgcggcga960
ttaaatctcgcgccgatcaactgggtgccagcgtggtggtgtcgatggtagaacgaagcg1020
gcgtcgaagcctgtaaagcggcggtgcacaatcttctcgcgcaacgcgtcagtgggctga1080
tcattaactatccgctggatgaccaggatgccattgctgtggaagctgcctgcactaatg1140
ttccggcgttatttcttgatgtctctgaccagacacccatcaacagtattattttctccc1200
atgaagacggtacgcgactgggcgtggagcatctggtcgcattgggtcaccagcaaatcg1260
cgctgttagcgggcccattaagttctgtctcggcgcgtctgcgtctggctggctggcata1320
aatatctcactcgcaatcaaattcagccgatagcggaacgggaaggcgactggagtgcca1380
tgtccggttttcaacaaaccatgcaaatgctgaatgagggcatcgttcccactgcgatgc1440
tggttgccaacgatcagatggcgctgggcgcaatgcgcgccattaccgagtccgggctgc1500
gcgttggtgcggatatctcggtagtgggatacgacgataccgaagacagctcatgttata1560
tcccgccgttaaccaccatcaaacaggattttcgcctgctggggcaaaccagcgtggacc1620
gcttgctgcaactctctcagggccaggcggtgaagggcaatcagctgttgcccgtctcac1680
tggtgaaaagaaaaaccaccctggcgcccaatacgcaaaccgcctctccccgcgcgttgg1740
ccgattcattaatgcagctggcacgacaggtttcccgactggaaagcgggcagtgagcgc1800
aacgcaattaatgtaagttagctcactcattaggcaccgggatctcgaccgatgcccttg1860
agagccttcaacccagtcagctccttccggtgggcgcggggcatgactatcgtcgccgca1920
cttatgactgtcttctttatcatgcaactcgtaggacaggtgccggcagcgctctgggtc1980
attttcggcgaggaccgctttcgctggagcgcgacgatgatcggcctgtcgcttgcggta2040
ttcggaatcttgcacgccctcgctcaagccttcgtcactggtcccgccaccaaacgtttc2100
ggcgagaagcaggccattatcgccggcatggcggccccacgggtgcgcatgatcgtgctc2160
ctgtcgttgaggacccggctaggctggcggggttgccttactggttagcagaatgaatca2220
ccgatacgcgagcgaacgtgaagcgactgctgctgcaaaacgtctgcgacctgagcaaca2280
acatgaatggtcttcggtttccgtgtttcgtaaagtctggaaacgcggaagtcagcgccc2340
tgcaccattatgttccggatctgcatcgcaggatgctgctggctaccctgtggaacacct2400
acatctgtattaacgaagcgctggcattgaccctgagtgatttttctctggtcccgccgc2460
atccataccgccagttgtttaccctcacaacgttccagtaaccgggcatgttcatcatca2520
gtaacccgtatcgtgagcatcctctctcgtttcatcggtatcattacccccatgaacaga2580
aatcccccttacacggaggcatcagtgaccaaacaggaaaaaaccgcccttaacatggcc2640
cgctttatcagaagccagacattaacgcttctggagaaactcaacgagctggacgcggat2700
gaacaggcagacatctgtgaatcgcttcacgaccacgctgatgagctttaccgcagctgc2760
ctcgcgcgtttcggtgatgacggtgaaaacctctgacacatgcagctcccggagacggtc2820
acagcttgtctgtaagcggatgccgggagcagacaagcccgtcagggcgcgtcagcgggt2880
gttggcgggtgtcggggcgcagccatgacccagtcacgtagcgatagcggagtgtatact2940
ggcttaactatgcggcatcagagcagattgtactgagagtgcaccatatatgcggtgtga3000
aataccgcacagatgcgtaaggagaaaataccgcatcaggcgctcttccgcttcctcgct3060
cactgactcgctgcgctcggtcgttcggctgcggcgagcggtatcagctcactcaaaggc3120
ggtaatacggttatccacagaatcaggggataacgcaggaaagaacatgtgagcaaaagg3180
ccagcaaaaggccaggaaccgtaaaaaggccgcgttgctggcgtttttccataggctccg3240
cccccctgacgagcatcacaaaaatcgacgctcaagtcagaggtggcgaaacccgacagg3300
actataaagataccaggcgtttccccctggaagctccctcgtgcgctctcctgttccgac3360
cctgccgcttaccggatacctgtccgcctttctcccttcgggaagcgtggcgctttctca3420
tagctcacgctgtaggtatctcagttcggtgtaggtcgttcgctccaagctgggctgtgt3480
gcacgaaccccccgttcagcccgaccgctgcgccttatccggtaactatcgtcttgagtc3540
caacccggtaagacacgacttatcgccactggcagcagccactggtaacaggattagcag3600
agcgaggtatgtaggcggtgctacagagttcttgaagtggtggcctaactacggctacac3660
tagaaggacagtatttggtatctgcgctctgctgaagccagttaccttcggaaaaagagt3720
tggtagctcttgatccggcaaacaaaccaccgctggtagcggtggtttttttgtttgcaa3780
gcagcagattacgcgcagaaaaaaaggatctcaagaagatcctttgatcttttctacggg3840
gtctgacgctcagtggaacgaaaactcacgttaagggattttggtcatgagattatcaaa3900
aaggatcttcacctagatccttttaaattaaaaatgaagttttaaatcaatctaaagtat3960
atatgagtaaacttggtctgacagttaccaatgcttaatcagtgaggcacctatctcagc4020
gatctgtctatttcgttcatccatagttgcctgactccccgtcgtgtagataactacgat4080
acgggagggcttaccatctggccccagtgctgcaatgataccgcgagacccacgctcacc4140
ggctccagatttatcagcaataaaccagccagccggaagggccgagcgcagaagtggtcc4200
tgcaactttatccgcctccatccagtctattaattgttgccgggaagctagagtaagtag4260
ttcgccagttaatagtttgcgcaacgttgttgccattgctgcaggcatcgtggtgtcacg4320
ctcgtcgtttggtatggcttcattcagctccggttcccaacgatcaaggcgagttacatg4380
atcccccatgttgtgcaaaaaagcggttagctccttcggtcctccgatcgttgtcagaag4440
taagttggccgcagtgttatcactcatggttatggcagcactgcataattctcttactgt4500
catgccatccgtaagatgcttttctgtgactggtgagtactcaaccaagtcattctgaga4560
atagtgtatgcggcgaccgagttgctcttgcccggcgtcaatacgggataataccgcgcc4620
acatagcagaactttaaaagtgctcatcattggaaaacgttcttcggggcgaaaactctc4680
aaggatcttaccgctgttgagatccagttcgatgtaacccactcgtgcacccaactgatc4740
ttcagcatcttttactttcaccagcgtttctgggtgagcaaaaacaggaaggcaaaatgc4800
cgcaaaaaagggaataagggcgacacggaaatgttgaatactcatactcttcctttttca4860
atattattgaagcatttatcagggttattgtctcatgagcggatacatatttgaatgtat4920
ttagaaaaataaacaaataggggttccgcgcacatttccccgaaaagtgccacctgaaat4980
tgtaaacgttaatattttgttaaaattcgcgttaaatttttgttaaatcagctcattttt5040
taaccaataggccgaaatcggcaaaatcccttataaatcaaaagaatagaccgagatagg5100
gttgagtgttgttccagtttggaacaagagtccactattaaagaacgtggactccaacgt5160
caaagggcgaaaaaccgtctatcagggcgatggcccactacgtgaaccatcaccctaatc5220
aagttttttggggtcgaggtgccgtaaagcactaaatcggaaccctaaagggagcccccg5280
atttagagcttgacggggaaagccggcgaacgtggcgagaaaggaagggaagaaagcgaa5340
aggagcgggcgctagggcgctggcaagtgtagcggtcacgctgcgcgtaaccaccacacc5400
cgccgcgcttaatgcgccgctacagggcgcgtcccattcgcca5443
<210>4
<211>579
<212>dna
<213>artificial
<400>4
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttacc60
attacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggt120
cgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccggaaggcgaa180
gttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacggc240
gcaagccagctgaataccggttatattgtcggctgccaggttagtattggcgacgacgca300
attagcgcaggtctgtctggcggtattgatctggaaggcggtagcattggcggtagtatt360
ggtctggatctgggtccgggggacgttaaatttgttcagatcgactacaaagacatcacc420
aaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggttgcgca480
ggttacgcacaggcacgcagctataccgttgtcgaaattatcggggatcactatagcaaa540
accaccctgtacggtatgccgtttagtatcggtctcgag579
<210>5
<211>597
<212>dna
<213>artificial
<400>5
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctgac60
ggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatgggc120
gcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttccggc180
ggcggtgaagacgttggcggcaaaatttatccgggttatgtggtcggctgccaggttaac240
attgacggtggtggcgtagaaggcggcgttgaaggttctgcagattggtctggcgatacc300
gttaccggtggtgtaggcgcagaatctggcggcgaactgaccctgggtccgggtcaagca360
aaaagcttctacatcctggacatcgagaaaccggacgattacggtaacgaagatcacgcg420
accaacaacaaattcaaaggcaacagcggcagcgtcacctgggcagatagtaccattggc480
ctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaaagtcaaagtcgagacc540
gacaacgtcatgtctgttgttacgctgtggggtcaaccgtttagtctgggtctcgag597
<210>6
<211>588
<212>dna
<213>artificial
<400>6
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttacc60
attacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggt120
cgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccggaaaggcga180
aagttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacg240
gcgcaagccagctgaataccggttatattgtcggctgccaggttagtattggcgacgcga300
cgcgcaattagcgcaggtctgtctggcggtattgatctggaaggcggtagcattggcggt360
agtattggtctggatctgggtccgggggacgttaaatttgttcagatcgactacaaagac420
atcaccaaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggt480
tgcgcaggttacgcacaggcacgcagctataccgttgtcgaaattatcggggatcgccac540
tatagcaaaaccaccctgtacggtatgccgtttagtatcggtctcgag588
<210>7
<211>619
<212>dna
<213>artificial
<400>7
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctgac60
cgtggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatg120
ggcgcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttcc180
ggcggcggtgaaagaccgtgttggcggcaaaatttatccgggttatgtggtcggctgcca240
ggttaacattgacggtggtggcgtagaaggcggcgttgaaaggttctgcagatcgttggt300
ctggcgatcgtaccgttaccggtggtgtaggcgcagaaatctggcggcgaaactgaccct360
gggtccgggtcaagcaaaaagcttctacatcctggacatcgagaaaccggacgattacgg420
taacgaagatcacgcgaccaacaacaaattcaaaggcaacagcggcagcgtcacctgggc480
agatagtaccattggcctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaa540
agtcaaagtcgagaaaaccgaccgtaacgtcatgtctgttgttacgctgtggggtcaacc600
gtttagtctgggtctcgag619
<210>8
<211>579
<212>dna
<213>artificial
<400>8
gaattcatggatacctttgttccgctgccggacggtcaaaaagttggtccgggcgttacc60
attacccgtaccggtgaacacgcagttatttctccgagtatggcagcaaacggcgcaggt120
cgcgttgcttgggtttctggtaacgcaaccgcagacgtaaccgttaccccgaaaggcaaa180
gttggtccgaataacggtccggcaggcgatccgggtaccaataatagtagtacccacggc240
gcaagccagctgaataccggttatattgtcggctgccaggttagtattggccgccgcgca300
attagcgcaggtctgtctggcggtattcgcctgaaaggcggtagcattggcggtagtatt360
ggtctgcgcctgggtccgggggacgttaaatttgttcagatcgactacaaagacatcacc420
aaaccgggcgtttacagcgtcgaataccaggacgtcgaaattcagattcagggttgcgca480
ggttacgcacaggcacgcagctataccgttgtcgaaattatcgggcgccactatagcaaa540
accaccctgtacggtatgccgtttagtatcggtctcgag579
<210>9
<211>597
<212>dna
<213>artificial
<400>9
gaattcatggatacctttgttccgctgccgggcggcgaaattaccaaaaccctgtctcgt60
ggcaccgttgttaccgtacgtctggttggcgaatctgcaaccatttctccgagtatgggc120
gcaaccccggttcatcgtaacgcttgggtttctggtagcgcacaagttgaaatttccggc180
ggcggtaaacgtgttggcggcaaaatttatccgggttatgtggtcggctgccaggttaac240
attcgtggtggtggcgtaaaaggcggcgttaaaggttctgcacgttggtctggccgtacc300
gttaccggtggtgtaggcgcaaaatctggcggcaaactgaccctgggtccgggtcaagca360
aaaagcttctacatcctgcgtatcaaaaaaccgcgtcgttacggtaacgaagatcacgcg420
accaacaacaaattcaaaggcaacagcggcagcgtcacctgggcagatagtaccattggc480
ctgtcaggttgtgctggttacgcacaagcacgttctttcgtcaaagtcaaagtcaaaacc540
cgtaacgtcatgtctgttgttacgctgtggggtcaaccgtttagtctgggtctcgag597
<210>10
<211>188
<212>prt
<213>artificial
<400>10
aspthrphevalproleuproaspglyglnlysvalglyproglyval
151015
thrilethrargthrglygluhisalavalileserprosermetala
202530
alaasnglyalaglyargvalalatrpvalserglyasnalathrala
354045
aspvalthrvalthrprogluglygluvalglyproasnasnglypro
505560
alaglyaspproglythrasnasnserserthrhisglyalasergln
65707580
leuasnthrglytyrilevalglycysglnvalserileglyasnasn
859095
alaileseralaglyleuserglyglyileaspleugluglyglyser
100105110
ileglyglyserileglyleuaspleuglyproglyaspvallysphe
115120125
valglnileasptyrlysaspilethrlysproglyvaltyrserval
130135140
glutyrglnaspvalgluileglnileglnglycysalaglytyrala
145150155160
glnalaargsertyrthrvalvalgluileileglyasphistyrser
165170175
lysthrthrleutyrglymetpropheserilegly
180185
<210>11
<211>194
<212>prt
<213>artificial
<400>11
aspthrphevalproleuproglyglygluilethrlysthrleuser
151015
aspglythrvalvalthrvalargleuvalglygluseralathrile
202530
serprosermetglyalathrprovalhisargasnalatrpvalser
354045
glyseralaglnvalgluileserglyglyglygluaspvalglygly
505560
lysiletyrproglytyrvalvalglycysglnvalasnileaspgly
65707580
glyglyvalgluglyglyvalglnglyseralaasntrpserglyasn
859095
thrvalthrglyglyvalglyalaglnserglyglyglnleuthrleu
100105110
glyproglyglnalalysserphetyrileleuaspileglulyspro
115120125
aspasptyrglyasngluasphisalathrasnasnlysphelysgly
130135140
asnserglyservalthrtrpalaaspserthrileglyleusergly
145150155160
cysalaglytyralaglnalaargserphevallysvallysvalglu
165170175
thraspasnvalmetservalvalthrleutrpglyglnpropheser
180185190
leugly
- 还没有人留言评论。精彩留言会获得点赞!