一种人ATP7b基因外显子PCR扩增系统、检测试剂盒及其应用的方法与流程
本发明属于人核酸体外检测技术领域,具体涉及人atp7b基因21个外显子pcr扩增及其应用。
背景技术
肝豆状核变性(hepatolenticulardegeneration,hld或wilsondisease,wd)是一种常染色体隐性遗传性铜代谢障碍病,以铜代谢障碍引起的肝硬化、基底节损害为主的脑变性疾病为特点。肝豆状核变性在世界范围内的发病率在15~25/100万,杂合子频率约1:100。肝豆状核性变是少数可以干预、治疗的遗传代谢疾病,早期发现,早期诊断和早期治疗对于症状前患者、临床出现症状患者预后有极其重要意义。
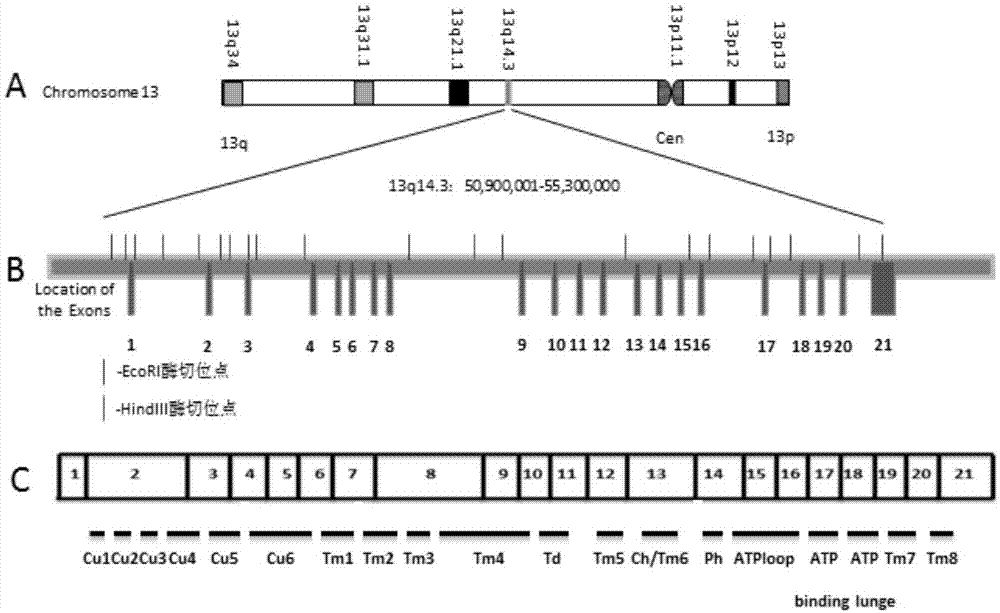
目前已经明确wd基因(atp7b)定位于13q14.3(图1.a),基因全长4.2kb,含有21个外显子(图1.b)和20个内含子,其cdna编码由1411氨基酸组成的p型cu转运atp酶(atp7base)(图1.c),参与cu的跨膜转运过程,故又称为atp7b基因,atp7b基因以点突变为主,已发现600多种突变,大多是杂合突变。
atp7b基因内一个或多个外显子突变是导致肝豆状核变性的根本原因,在国内外的诸多研究显示,atp7b基因突变呈现地域差异及人种差异。在欧美国家,肝豆状核性变基因exon14第1069位密码子突变是一个典型的热点突变,突变频率高达68.3%,而国内学者对中国wd患者基因突变研究显示exon8的arg778leu突变频率高达60%,为公认的第一突变热点。
目前关于atp7b基因突变的检测方法,国内外常用的分子检测方法有:sanger测序和dhplc。sangersequencing是通过设计atp7b基因的21个外显子或部分已知的突变热点外显子区域引物,以基因组dna为模板进行常规pcr,pcr产物经过琼脂糖电泳确认电泳条带后进行一代测序,测序结果与参考序列进行比对,最终确认目标扩增区域是否具有突变发生,该方法目前也是被认定为wd患者基因检测的金标准。在此方法基础上进行设计的如pcr-rflp、str等方法也常常被用于atp7b基因的联合分析。
变性高效液相色谱(denaturinghighperformanceliquidchromatography,dhplc)是一种高通量筛选dna序列变异的新技术,dhplc是近来发展起来探索人类基因组dna序列变异的新手段,亦称为温度调节的杂合双链分析(tmha)。它利用在部分变性条件下同源、异源双链dna解链特征的差异进行变异检测。可以敏感而准确地发现dna变异,能自动化操作,并能在数分钟内快速获取实验数据,且不存在假阳性或假阴性的问题,适用于大量人群筛选。该技术的高准确性和高敏感性在多种基因微小突变及多态性(snps)的研究中得到证实,因此,对于atp7b这样一个异质性基因来说,dhplc为一个理想方法,在实际临床检测方面应用较广。
技术实现要素:
本发明的目的在于提供一种成本低、效率高、覆盖全的能够对人atp7b基因进行突变检测的扩增系统,以及atp7b基因突变筛查,辅以肝豆状核变性致病的诊断分析。
本发明第一方面提供了一种对用于人atp7b基因21个外显子的pcr扩增系统,所述扩增系统包含以下外显子位点相对应的23对引物:
位点exon1,相对应的引物序列为seqidno.1和seqidno.2;位点exon2-1,相对应的引物序列为seqidno.3和seqidno.4;位点exon2-2,相对应的引物序列为seqidno.5和seqidno.6;位点exon2-3,相对应的引物序列为seqidno.7和seqidno.8;位点exon3,相对应的引物序列为seqidno.9和seqidno.10;位点exon4,相对应的引物序列为seqidno.11和seqidno.12;位点exon5,相对应的引物序列为seqidno.13和seqidno.14;位点exon6,相对应的引物序列为seqidno.15和seqidno.16;位点exon7,相对应的引物序列为seqidno.17和seqidno.18;位点exon8,相对应的引物序列为seqidno.19和seqidno.20;位点exon9,相对应的引物序列为seqidno.21和seqidno.22;位点exon10,相对应的引物序列为seqidno.23和seqidno.24;位点exon11,相对应的引物序列为seqidno.25和seqidno.26;位点exon12,相对应的引物序列为seqidno.27和seqidno.28;位点exon13,相对应的引物序列为seqidno.29和seqidno.30;位点exon14,相对应的引物序列为seqidno.31和seqidno.32;位点exon15,相对应的引物序列为seqidno.33和seqidno.34;位点exon16,相对应的引物序列为seqidno.35和seqidno.36;位点exon17,相对应的引物序列为seqidno.37和seqidno.38;位点exon18,相对应的引物序列为seqidno.39和seqidno.40;位点exon19,相对应的引物序列为seqidno.41和seqidno.42;位点exon20,相对应的引物序列为seqidno.43和seqidno.44;位点exon21,相对应的引物序列为seqidno.45和seqidno.46。
上述23对引物覆盖99%以上的atp7b基因突变(缺失、重复、碱基突变等),该23个位点相应的pcr扩增引物的信息详见表1。
表1.21个外显子46条pcr扩增引物信息
本发明所述的pcr扩增系统中,引物由seqidno.1至seqidno.46所示寡核苷酸序列的pcr扩增引物的干粉或溶液组成。所述23对pcr扩增引物的工作液浓度为50~400nmol/l。
本发明第二方面提供了本发明第一方面所述pcr扩增系统在制备对人atp7b基因21个外显子检测的试剂盒的用途。
本发明第三方面提供了一种对人atp7b基因21个外显子检测的试剂盒,其包含含有本发明第一方面所述pcr扩增系统的引物组合物容器和pcr反应母液容器;其中:
所述引物组合物容器包含序列为seqidno.1至seqidno.46所示的引物的贮存液,贮存液中各引物的浓度为相应引物工作液浓度的2~10倍;
所述pcr反应母液容器内含有进行pcr反应的2~5倍反应浓度的pcr反应母液,pcr反应母液包含酶活为0.5~5u的dna聚合酶、浓度为1~5mmol/l的镁离子、浓度为40~400μmol/l的dntp及浓度为20~100mmol/l的tris-hcl缓冲液。
本发明第四方面提供了一种本发明第三方面所述试剂盒的使用方法,具体如下:
(1)多重pcr扩增:总反应体系为20μl,反应体系组成如下:
(2)pcr反应在普通pcr仪进行,pcr反应条件如下:95℃10分钟启动后,94℃30秒、60℃45秒、72℃45秒,共32个循环,然后70℃延伸10分钟,最后4℃保温;
(3)pcr产物取10μl,按常规操作在琼脂糖凝胶电泳仪上进行横向电泳,得到每一个外显子pcr扩增产物的凝胶电泳图谱。
在另一优选例中,所述基因组dna为人外周血dna。
本发明第五方面提供了本发明第三方面所述试剂盒在非诊断性进行人atp7b基因21个外显子检测中的用途。
本发明的有益效果:
依据本发明,实现了一次pcr反应同时完成所述人atp7b基因的21个外显子检测,本研究旨在建立肝豆状核变性(wilsondisease,wd)atp7b基因外显子突变的检测方法,通过扩增目标外显子片段区域后进行sanger测序,比对目标区域参考序列进而对基因突变发生与否做出判断,以期从分子水平达到快速诊断的目的,为wd患者的早发现或早干预提供指导依据。
附图说明
图1为atp7b基因外显子分布及表达蛋白示意图。
图2为本发明试剂盒检测正常母亲样本atp7b基因外显子琼脂糖电泳图,电泳显示21个外显子均出现对应pcr片段的目的条带。
图3为本发明试剂盒检测患病小孩样本atp7b基因外显子琼脂糖电泳图,电泳显示21个外显子均出现对应pcr片段的目的条带。
图4为atp7b基因1号外显子测序结果比对结果,结果显示无突变。
具体实施方式
为更好的理解本发明的内容,下面以正常母亲基因组dna和患病小孩基因组dna为样本对本检测方法具体实施例作进一步说明。应理解,下列具体实施例仅用于说明本发明,而不是对本发明的限制。
本发明pcr反应体系试剂中的引物组合物所包括的核苷酸序列为seqidno.1至seqidno.46的引物为发明人通过引物设计,由dna合成公司按照本领域所通用的常规合成方法合成的,然后将其配制为工作浓度50~400nmol/l。
在本实施例中扩增反应在abi9700热循环仪上进行,电泳后pcr产物在abi3170遗传分析仪上进行测序。所使用其它试剂和材料如内标、电泳缓冲液、pop7、hi-di均为本领域技术人员常用的常规材料。
实施例
1:dna提取后测定od值及浓度:
dna按照相关提取试剂盒的操作提取后进行od值测定,要求:1.6≤od260/od280≤2.0,dna浓度稀释至10.0ng/μl的工作浓度备检。
2:pcr体系配制
按以下体系配制pcr反应体系(总反应体系为20μl):
在试剂盒中取出引物容器、pcr反应母液容器。按总反应数乘以上述反应体系中单个反应需要量分别计算出所需要的pcr反应母液量、引物量和ddh2o量,在一个1.5mlep管中将上述试剂混均匀,在按每个pcr反应管19μl进行分装、编号,然后按样本编号分别加入样本dna模板2.5μl,并再次混匀。
3:pcr反应
采用abi9700pcr仪进行pcr反应。
pcr条件如下:95℃10分钟启动后,94℃30秒、60℃45秒、72℃45秒,共32个循环,然后72℃延伸10分钟,最后4℃保温。
4:电泳检测
(1)制胶:取1.6g琼脂糖粉末加入80mltae(1×)缓冲液中,轻摇混匀后中火煮沸2次,待冷却温度50℃附件加入核酸染料godview,充分摇匀后倒入事前准备好的胶槽内,插上胶梳静置。
(2)点样:取1μlloadingbuffer加入10μlpcr产物中混匀,全部加到胶孔内。
(3)电泳:将电泳仪设置为恒压稳流(500ma)状态,电压125v,电泳时间25分钟。
(4)结果:观察电泳条带是否出现各自对应目的片段。
5:测序验证
经过琼脂糖凝胶电泳检测后的电泳条带的确认,对各自atp7b基因外显子的pcr产物对应条带进行回收(或pcr产物剩余量)进行一代测序,将测序结果与数据库(ncbi、ucsc)的参考序列进行比对(软件vectornit-alignx),对测序结果有无突变做直观的判断并借助wilsondiseasemutationdatabase权威数据库对突变位点进行查询,明确突变位点的临床意义。
6:数据分析
经过序列比对及数据库突变信息的查询对检测样本的atp7b基因21个外显子进行统计(表2,表3)。
表2.正常母亲样本的atp7b基因21个外显子突变信息表
表3.患病小孩样本的atp7b基因21个外显子突变信息表
从图2可以看出电泳显示21个外显子均出现对应pcr片段的目的条带。
阴性对照:ntc反应孔的pcr产物电泳通道显示无带,显示该批次pcr实验操作环节未受污染,为正常结果。
阳性对照:pos反应孔的pcr产物电泳通道显示有目的片段大小的电泳条带,显示该批次pcr实验体系有效,为正常结果。
反应组1-21:atp7b基因21个外显子反应孔的pcr产物电泳通道显示有各自的片段大小的电泳条带,显示目标扩增区域未出现缺失现象。
m:琼脂糖电泳的marker,大小标识。
结论:pcr扩增产物的琼脂糖电泳未发现缺失,需进行测序确认。
从图3可以看出电泳显示21个外显子均出现对应pcr片段的目的条带。
阴性对照:ntc反应孔的pcr产物电泳通道显示无带,显示该批次pcr实验操作环节未受污染,为正常结果。
阳性对照:pos反应孔的pcr产物电泳通道显示有目的片段大小的电泳条带,显示该批次pcr实验体系有效,为正常结果。
反应组1-21:atp7b基因21个外显子反应孔的pcr产物电泳通道显示有各自的片段大小的电泳条带,显示目标扩增区域未出现缺失现象。
m:琼脂糖电泳的marker,大小标识。
结论:pcr扩增产物的琼脂糖电泳未发现缺失,需进行测序确认。
本发明所提出的人atp7b基因的突变检测方法及应用可在具有pcr仪以及遗传分析的实验室稳定实施,检测时间为4~6小时。同时,本发明所提供的试剂可以方便地在生物技术公司生产以及在生物医学检测机构、专业医疗机构用于检测,具备产业化以及推广应用的条件。
本发明已参照其特定的实施例作了描述。对于本领域技术人员而言,依据前面的描述,可能对本发明做各种修改或变换,包括(但不仅限于):依据各遗传标记扩增片段范围改变检测的分组排布,依据其它的pcr反应母液对pcr扩增条件、引物反应浓度进行优化,以及改变所推荐的反应体系等。很显然,上述修改或变换对于本领域技术人员而言都是可能的,但这些修改和变换并不背离本发明的精神和范围。
序列表
<110>上海五色石医学研究股份有限公司
<120>一种人atp7b基因外显子pcr扩增系统、检测试剂盒及其应用的方法
<130>z001039180041cn
<160>46
<170>patentinversion3.5
<210>1
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>1
cactctgcgcctcctctcccg21
<210>2
<211>19
<212>dna
<213>人工序列(artificialsequence)
<400>2
tcggccttccctgcgcacc19
<210>3
<211>27
<212>dna
<213>人工序列(artificialsequence)
<400>3
agaagctgggatgttgtagaaaatatt27
<210>4
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>4
aatggagctgacacaggactg21
<210>5
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>5
ctggccctcaaggtccttgc20
<210>6
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>6
ctgggctggtacaagaagggtca23
<210>7
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>7
atattggccagctcctagggg21
<210>8
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>8
accatccaggagctataagacacaa25
<210>9
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>9
ctcaccaagagccctgaaacc21
<210>10
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>10
ttgctgggtattctgaagggag22
<210>11
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>11
gatgtgtttctttgttcggtta22
<210>12
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>12
aacaacaacaaaccagacacg21
<210>13
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>13
gctgcctgttacctagactcc21
<210>14
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>14
ccatgggaaaagttgaagaatt22
<210>15
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>15
aacccacaaagtctactgaggc22
<210>16
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>16
acaagaccagctggcagagt20
<210>17
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>17
cagacatgtgacaaaggcagg21
<210>18
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>18
aagtgccatttaaaccaagct21
<210>19
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>19
tccctacttgctggcagc18
<210>20
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>20
aaacatggtgttcagaggaagtg23
<210>21
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>21
tgtttctctcgcaccagctgt21
<210>22
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>22
tgtcaatacaacatgggcatctg23
<210>23
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>23
ctattgtaacagctggcctagaacc25
<210>24
<211>19
<212>dna
<213>人工序列(artificialsequence)
<400>24
ctgtcacttgctcagcccc19
<210>25
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>25
gctgtcaggtcacatgagtgc21
<210>26
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>26
ctgatttcccagaactcttcacat24
<210>27
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>27
gtgactgtttatcctactctggctt25
<210>28
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>28
ataggttgtaatttcccatggtctt25
<210>29
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>29
actggtggctactctgttgctactg25
<210>30
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>30
tgaactctcaacctgcctctgac23
<210>31
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>31
agttctgcctcaggagtgtgac22
<210>32
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>32
cagctaggagagaaggacatgg22
<210>33
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>33
tgacccacctctacttttaaccag24
<210>34
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>34
tcctttctctcagttcccgct21
<210>35
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>35
gaaggatgactctgaactgccca23
<210>36
<211>26
<212>dna
<213>人工序列(artificialsequence)
<400>36
tcacaagaggtgcttacaaggttaca26
<210>37
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>37
cattgcaagtgtggtatcttggt23
<210>38
<211>19
<212>dna
<213>人工序列(artificialsequence)
<400>38
tacagctcagtgctgggcc19
<210>39
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>39
caagggtaacttgaggtttctgc23
<210>40
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>40
tcattctgatggagaggagcac22
<210>41
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>41
tgggcagaccccttcctcac20
<210>42
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>42
aagcctttctgggcgcagct20
<210>43
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>43
gcctgctcatggtgctgataa21
<210>44
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>44
ttctaggaagcctcactttggg22
<210>45
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>45
ggatgagaggccttcaccag20
<210>46
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>46
gtggtgagtggaggcaagtc20
- 还没有人留言评论。精彩留言会获得点赞!