用于结直肠癌及其癌前病变早期诊断、检测或筛查的引物探针组和试剂盒的制作方法
本发明属于生物医学领域,涉及一种用于结直肠癌及其癌前病变早期诊断、检测或筛查的粪便多基因联合检测引物探针组及试剂盒。
背景技术:
在西方国家,结直肠癌(crc,或称为大肠癌)是一个主要的健康问题。根据美国癌症协会的估计,crc在美国的死亡人数约为50000人,在2016年确诊了近130000例新病例,为第三种最常见的癌症,而在中国,结直肠癌发病率居高位,且呈上升趋势。当前结直肠癌的初治分期比例为:i期占15%;ii期占20%-30%;iii期占30%-40%;iv期占20%-25%。在生存期方面,i期患者的5年生存率可达90%以上,而iv期患者只有略大于10%的生存率。散发性结直肠癌是最常见的肠癌,占比95%(其余为遗传性结直肠癌)。从正常肠粘膜发展为肠癌有三个主要途径:腺瘤性息肉-癌途径,约占50%-70%;锯齿状息肉-癌变途径,约占30%-35%;非息肉途径癌变,约占3%-5%。腺瘤是肠癌的主要癌前疾病,占比85%甚至更高,是肠癌预防的第一线。因此,实现结直肠腺癌的早期筛查从而达到早诊断早治疗对于提高患者的生存率进而提升全面健康水平有着重要意义。
目前结直肠癌检测方法有很多种,如粪便隐血试验、结直肠镜镜检、计算机扫描断层成像(ct)或粪便dna检测,以上方法目前都得到了一定的应用,但也都存在一定的缺陷。结直肠镜镜检是目前结直肠癌筛查中灵敏度最高的方法,但是该方法要求专业的操作者进行操作,同时该方法价格昂贵,而且作为一种侵入性的检测方法,患者的接受度比较低,因此在早期筛查结直肠癌上存在一定的缺陷。粪便隐血试验作为一种快速检测方法,在结直肠癌筛查中也有广泛的应用,但是该方法特异性较低,导致存在大量的假阳性,而且检测结果易受饮食和药物的干扰,同时还需要多次采样检测,因此成为患者弃检率非常高的检测项目。其它方法如ct只能检测到中晚期的癌症,因此无法在早期筛查中应用。粪便是直接来源于结直肠的生物样本,粪便中包含着大量的结直肠脱落的基因组dna,特别是在结直肠息肉和肿瘤发生时会有更多的dna脱落,因此采用粪便dna进行结直肠肿瘤无创早期筛查是一种非常有效的手段。当前,美国fda批准的fit+粪便dna多靶标dna检测,可以检出92%的结直肠癌和43%进展期腺瘤,是美国癌症协会结直肠癌筛查指南推荐的筛查方法,但是该方法价格高达600多美金,而且在检测过程中需要同时进行多个反应检测,因此操作也十分复杂,并不适合像中国这样的发展中国家应用。
非正常dna甲基化与很多疾病的发生和维持有着紧密联系,特别是近年来的研究成果表明dna甲基化在癌症的诱发和维持中起着重要作用,使之成为很多癌症的很好的生物标志物。sept9是一种非常有效的癌症dna甲基化标记物,已有研究证明setp9在结直肠癌组织和正常组织中呈现明显的表达差异。sept9血液甲基化检测已经被fda和cfda批准用于结直肠癌早期筛查和辅助诊断,但是该方法对结直肠癌灵敏度仅为60-70%,对i期结直肠癌的检出率不足50%,对进展期腺瘤的检出率约为10%,因此在结直肠癌早期筛查上存在一定的缺陷。
技术实现要素:
本发明的目的在于提供一种用于结直肠癌及其癌前病变早期诊断、检测或筛查的粪便多基因联合检测引物探针组和试剂盒,以解决现有技术中存在的上述全部缺陷或缺陷之一。
为实现上述目的,一方面,本发明提供了一种用于结直肠癌及其癌前病变早期诊断、检测或筛查的引物探针组,包括选自以下各组引物和探针中的至少两组:a)甲基化的sdc2基因的正向引物、反向引物、blocker引物和探针,b)甲基化的sfrp2基因的正向引物、反向引物、blocker引物和探针、c)甲基化的sfrp1基因的正向引物、反向引物、blocker引物和探针、d)甲基化的sept9基因的正向引物、反向引物、blocker引物和探针以及e)甲基化的prima1基因的正向引物、反向引物、blocker引物和探针。
进一步地,所述甲基化的sdc2基因的正向引物选自序列表中seqidno:1~3所示的任一种、反向引物选自序列表中seqidno:4~6所示的任一种、blocker引物选自序列表中seqidno:7~9所示的任一种、探针选自序列表中seqidno:10~12所示的任一种;所述甲基化的sfrp2基因的正向引物选自序列表中seqidno:13~15所示的任一种、反向引物选自序列表中seqidno:16~18中的任一种、blocker引物选自序列表中seqidno:19~21所示的任一种、探针选自序列表中seqidno:22~24所示的任一种;所述甲基化的sfrp1基因的正向引物选自序列表中seqidno:25~27所示的任一种、反向引物选自序列表中seqidno:28~30所示的任一种、blocker引物选自序列表中seqidno:31~33所示的任一种、探针选自序列表中seqidno:34~36所示的任一种;所述甲基化的sept9基因的正向引物选自序列表中seqidno:37~39所示的任一种、反向引物选自序列表中seqidno:40~42所示的任一种、blocker引物选自序列表中seqidno:43~45所示的任一种、探针选自序列表中seqidno:46~48所示的任一种;所述甲基化的prima1基因的正向引物选自序列表中seqidno:49~51所示的任一种、反向引物选自序列表中seqidno:52~54所示的任一种、blocker引物选自序列表中seqidno:55~57所示的任一种、探针选自序列表中seqidno:58~60所示的任一种。
进一步地,检测对象为从人源粪便中经过基因组dna提取后再使用亚硫酸氢盐转化及纯化后得到的dna样本,检测方法为甲基化特异性pcr。
另一方面,本发明提供了上述用于结直肠癌及其癌前病变早期诊断、检测或筛查的引物探针组在制备检测结直肠癌或结直肠癌前病变产品中的应用。所述的结直肠癌前病变为结直肠腺瘤。
另一方面,本发明提供了一种用于结直肠癌及其癌前病变早期诊断、检测或筛查的试剂盒,包括上述用于结直肠癌及其癌前病变早期诊断、检测或筛查的引物探针组。
进一步地,所述试剂盒还包含一组内参基因的正向引物、反向引物和探针,其中所述内参基因为actb,所述actb的正向引物如序列表中seqidno:61所示、反向引物如序列表中seqidno:62所示,探针如序列表中seqidno:63所示。
进一步地,所述试剂盒还包含4种dntp混合溶液、mg2+溶液、dna聚合酶、pcr反应缓冲液、pcr去离子水。
进一步地,所述试剂盒还包含阴性外质控,所述阴性外质控为sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因均呈现结直肠肿瘤和癌前病变特异性甲基化阴性的基因组序列或合成基因序列。
进一步地,所述试剂盒还包含阳性外质控,所述的阳性外质控为sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因均呈现结直肠肿瘤和癌前病变特异性甲基化阳性的基因组序列或合成基因序列。
与现有技术相比,本发明具有以下优点:
本发明将多个与结直肠癌和结直肠进展期腺瘤特异的甲基化标记物在1管pcr中同时检测,既能提高结直肠癌或其癌前病变的检测灵敏度也能最大程度降低操作繁复程度,为结直肠癌无创早期筛查提供了一种有效手段。
附图说明
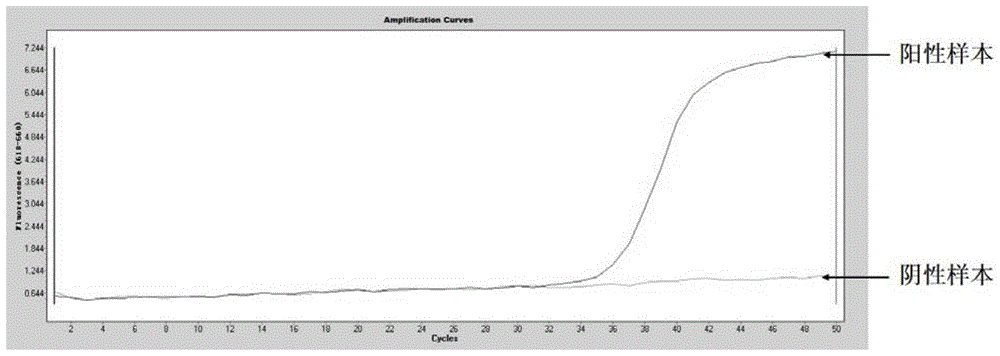
图1示出了实施例1中sdc2甲基化引物探针组检测结直肠癌甲基化阳性样本和阴性样本的结果;
图2示出了实施例1中sfrp2甲基化引物探针组检测结直肠癌甲基化阳性样本和阴性样本的结果;
图3示出了实施例1中sfrp1甲基化引物探针组检测结直肠癌甲基化阳性样本和阴性样本的结果;
图4示出了实施例1中sept9甲基化引物探针组检测结直肠癌甲基化阳性样本和阴性样本的结果;
图5示出了实施例1中prima1甲基化引物探针组检测结直肠癌甲基化阳性样本和阴性样本的结果。
具体实施方式
下面结合具体实施例对本发明作进一步描述。以下实施例仅用于更加清楚地说明本发明的技术方案,而不能以此来限制本发明的保护范围。
一、试剂盒的组分:
1)各引物和探针的序列,见表1:
表1各引物和探针序列
2)pcr试剂:
4种dntp混合溶液、mg2+溶液、dna聚合酶、pcrbuffer、pcr去离子水。
3)阴性外质控
阴性外质控为sdc2基因,sfrp2基因,sfrp1基因,sept9基因和prima1基因均呈现结直肠肿瘤和癌前病变特异性甲基化阴性的基因组序列或合成基因序列。
4)阳性外质控
阳性外质控指sdc2基因,sfrp2基因,sfrp1基因,sept9基因和prima1基因均呈现结直肠肿瘤和癌前病变特异性甲基化阳性的基因组序列或合成基因序列。
二、试剂盒判别阳性判别标准
当actb基因有信号且甲基化的sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因中任意一个基因为阳性则该样本判别为阳性。
三、检测样本
检测样本为从人源粪便中经过基因组dna提取后再使用亚硫酸氢盐转化及纯化后得到的dna样本。
四、检测方法
检测方法采用甲基化特异性pcr。
下述实施例中所述试剂原料除特别注明来源外,均为市售的常见原料,试剂的配制采用常规方法。实施例中未详述的方法均为本领域常规方法和操作。
实施例1多甲基化标记物检测的有效性验证
1)选取甲基化的sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因5个基因的正向引物、反向引物、blocker引物和探针的序列如下:
sdc2:seqidno:1,4,7,10;sfrp2:seqidno:13,16,19,22;sfrp1:seqidno:25,28,31,34;sept9:seqidno:37,40,43,46;prima1:seqidno:49,52,55,58;
2)在上述选取的引物和探针中,加入如seqidno:61-63所示序列的内参基因actb的正向引物、反向引物和探针;然后加入0.4mm4种dntps混合溶液、5mmmg2+溶液、1.2xpcr反应缓冲液、0.1u/uldna聚合酶和pcr去离子水,同时检测结直肠癌甲基化阳性样本和阴性样本(结直肠癌甲基化阳性样本和阴性样本均为现有样本),结果如图1至5所示,该结果表明同时采用sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因5种甲基化标记物的试剂盒可有效检测结直肠癌。
实施例2结直肠癌和癌前病变粪便样本的检测
1)选取甲基化的sdc2基因、sfrp2基因、sfrp1基因、sept9基因和prima1基因5个基因的正向引物、反向引物、blocker引物和探针序列如下:
sdc2:seqidno:2,5,8,11;sfrp2:seqidno:14,17,20,23;sfrp1:seqidno:26,29,32,35;sept9:seqidno:38,41,44,47;prima1:seqidno:50,53,56,59;
2)在上述选取的引物和探针中,加入如seqidno:61-63所示序列的内参基因actb的正向引物、反向引物和探针;然后加入0.5mm4种dntps混合溶液、5mmmg2+溶液、1xpcrbuffer、0.1u/μldna聚合酶和pcr去离子水,同时检测结直肠癌和癌前病变粪便样本,检测结果如表2。其中,所有结直肠癌和癌前病变粪便样本均使用苏州唯善生物科技有限公司制造的粪便dna提取试剂盒提取后再使用亚硫酸氢盐转化试剂盒转化及纯化处理后得到。
表2结直肠癌和癌前病变粪便样本检测结果
由上表可以看出,通过5种甲基化标记物检测,对结直肠癌前病变检出率高达75%,对早期结直肠癌的检出率也接近90%,因此证明该方法是一种十分有效的结直肠癌或其癌前病变早期诊断、检测和筛查的方法。
以上已以较佳实施例公布了本发明,然其并非用以限制本发明,凡采取等同替换或等效变换的方案所获得的技术方案,均落在本发明的保护范围内。
序列表
<110>苏州唯善生物科技有限公司
<120>用于结直肠癌及其癌前病变早期诊断、检测或筛查的引物探针组和试剂盒
<130>wlx2019022801
<141>2019-02-28
<160>63
<170>siposequencelisting1.0
<210>1
<211>18
<212>dna
<213>homosapiens
<400>1
cgcgttttcggggcgtag18
<210>2
<211>18
<212>dna
<213>homosapiens
<400>2
ctacgccccgaaaacgcg18
<210>3
<211>18
<212>dna
<213>homosapiens
<400>3
ggaggaagcgagygtttt18
<210>4
<211>19
<212>dna
<213>homosapiens
<400>4
gtttcggattcgtgtgcgc19
<210>5
<211>19
<212>dna
<213>homosapiens
<400>5
gcgcacacgaatccgaaac19
<210>6
<211>20
<212>dna
<213>homosapiens
<400>6
cggattcgtgtgcgcgggtt20
<210>7
<211>24
<212>dna
<213>homosapiens
<400>7
gtaggtgtaggaggaggaagtgag24
<210>8
<211>24
<212>dna
<213>homosapiens
<400>8
ctcacttcctcctcctacacctac24
<210>9
<211>22
<212>dna
<213>homosapiens
<400>9
tttggggtgtagttgtgggtgg22
<210>10
<211>17
<212>dna
<213>homosapiens
<400>10
cccgccgcccgcaacta17
<210>11
<211>22
<212>dna
<213>homosapiens
<400>11
agttcgagttttcgagtttgag22
<210>12
<211>25
<212>dna
<213>homosapiens
<400>12
aactcgaaaactcgaactcgaaact25
<210>13
<211>22
<212>dna
<213>homosapiens
<400>13
gtcgtcgttcgttcgttttagg22
<210>14
<211>20
<212>dna
<213>homosapiens
<400>14
tcgtcgttcgttcgttttag20
<210>15
<211>18
<212>dna
<213>homosapiens
<400>15
aacgaaacgaccgaaatt18
<210>16
<211>21
<212>dna
<213>homosapiens
<400>16
cgcgaaataccctacgtaccc21
<210>17
<211>19
<212>dna
<213>homosapiens
<400>17
cgcgaaataccctacgtac19
<210>18
<211>20
<212>dna
<213>homosapiens
<400>18
gttagttttttggggtttcg20
<210>19
<211>29
<212>dna
<213>homosapiens
<400>19
atgtaccccccactcctgcaacctgtgcc29
<210>20
<211>19
<212>dna
<213>homosapiens
<400>20
tcctgcaacctgtgcccta19
<210>21
<211>34
<212>dna
<213>homosapiens
<400>21
atgtaccccccactcctgcaacctgtgccctact34
<210>22
<211>21
<212>dna
<213>homosapiens
<400>22
tcccgcaacccgcgccctact21
<210>23
<211>19
<212>dna
<213>homosapiens
<400>23
tcccgcaacccgcgcccta19
<210>24
<211>19
<212>dna
<213>homosapiens
<400>24
gaacttatcccgaacccgc19
<210>25
<211>22
<212>dna
<213>homosapiens
<400>25
gaagtcgaagaattgtatgatc22
<210>26
<211>22
<212>dna
<213>homosapiens
<400>26
gatcatacaattcttcgacttc22
<210>27
<211>24
<212>dna
<213>homosapiens
<400>27
agtagaagtcgaagaattgtatga24
<210>28
<211>20
<212>dna
<213>homosapiens
<400>28
cgtatcgctaactctacgaa20
<210>29
<211>20
<212>dna
<213>homosapiens
<400>29
ttcgtagagttagcgatacg20
<210>30
<211>20
<212>dna
<213>homosapiens
<400>30
cccgtatcgctaactctacg20
<210>31
<211>31
<212>dna
<213>homosapiens
<400>31
tgtatgattggtttgtatgagttgtgtatgg31
<210>32
<211>31
<212>dna
<213>homosapiens
<400>32
ccatacacaactcatacaaaccaatcataca31
<210>33
<211>38
<212>dna
<213>homosapiens
<400>33
ttgaagaattgtatgattggtttgtatgagttgtgtat38
<210>34
<211>20
<212>dna
<213>homosapiens
<400>34
ttcgtacgagtcgcgtacgg20
<210>35
<211>20
<212>dna
<213>homosapiens
<400>35
ccgtacgcgactcgtacgaa20
<210>36
<211>21
<212>dna
<213>homosapiens
<400>36
cggttcgtacgagtcgcgtac21
<210>37
<211>20
<212>dna
<213>homosapiens
<400>37
aaataatcccatccaactac20
<210>38
<211>20
<212>dna
<213>homosapiens
<400>38
gtagttggatgggattattt20
<210>39
<211>21
<212>dna
<213>homosapiens
<400>39
aaataatcccatccaactacg21
<210>40
<211>21
<212>dna
<213>homosapiens
<400>40
tcgtcgttgtttttcgcgcga21
<210>41
<211>21
<212>dna
<213>homosapiens
<400>41
tcgcgcgaaaaacaacgacga21
<210>42
<211>25
<212>dna
<213>homosapiens
<400>42
cataataactaataaacaacraatc25
<210>43
<211>24
<212>dna
<213>homosapiens
<400>43
ttggattttgtggttaatgtgtag24
<210>44
<211>26
<212>dna
<213>homosapiens
<400>44
tgttggattttgtggttaatgtgtag26
<210>45
<211>21
<212>dna
<213>homosapiens
<400>45
gttattatgttggattttgtg21
<210>46
<211>18
<212>dna
<213>homosapiens
<400>46
atttcgcggttaacgcgt18
<210>47
<211>18
<212>dna
<213>homosapiens
<400>47
acgcgttaaccgcgaaat18
<210>48
<211>18
<212>dna
<213>homosapiens
<400>48
gttaaccgcgaaatccga18
<210>49
<211>19
<212>dna
<213>homosapiens
<400>49
cggttgttcggggtattgg19
<210>50
<211>18
<212>dna
<213>homosapiens
<400>50
cggttgttcggggtattg18
<210>51
<211>19
<212>dna
<213>homosapiens
<400>51
ccaataccccgaacaaccg19
<210>52
<211>20
<212>dna
<213>homosapiens
<400>52
cccaacgaaaactccctacc20
<210>53
<211>18
<212>dna
<213>homosapiens
<400>53
caacgaaaactccctacc18
<210>54
<211>20
<212>dna
<213>homosapiens
<400>54
ggtagggagttttcgttggg20
<210>55
<211>17
<212>dna
<213>homosapiens
<400>55
ctgctgctacctcttgc17
<210>56
<211>29
<212>dna
<213>homosapiens
<400>56
ctactgatgcctcctgctgctacctcttg29
<210>57
<211>29
<212>dna
<213>homosapiens
<400>57
caagaggtagcagcaggaggcatcagtag29
<210>58
<211>20
<212>dna
<213>homosapiens
<400>58
ccgccgctacctctcgcgaa20
<210>59
<211>17
<212>dna
<213>homosapiens
<400>59
ccgccgctacctctcgc17
<210>60
<211>17
<212>dna
<213>homosapiens
<400>60
gcgagaggtagcggcgg17
<210>61
<211>23
<212>dna
<213>homosapiens
<400>61
gtgatggaggaggtttagtaagt23
<210>62
<211>24
<212>dna
<213>homosapiens
<400>62
ccaataaaacctactcctccctta24
<210>63
<211>28
<212>dna
<213>homosapiens
<400>63
ccaccacccaacacacaataacaaacac28
- 还没有人留言评论。精彩留言会获得点赞!