快速鉴定光皮梾木种群的分子检测方法与流程
本发明属于分子生物学技术领域,更具体地,本发明涉及一种快速鉴定光皮梾木种群的分子检测方法。
背景技术:
光皮梾木(cornuswilsonianawanger)又名光皮树、油树、狗骨木、斑皮抽水树等,属山茱萸科梾木属,是我国特有的多用途乡土木本油料树种。光皮梾木果油作为食用油已有100年历史,1981年经国家粮食部鉴定,光皮梾木油为一级食用油;2013年12月,国家卫生和计划生育委员会批准光皮梾木果实油为我国的新食品原料。动物和临床试验结果表明光皮梾木油可显著降低体内胆固醇,防治高血脂症,尤其是老年高血脂症,同时具有减肥功效。光皮梾木是一种兼有经济、生态和社会效益的重要油料树种。
但是,一般从表型特征很难区分光皮梾木的种群,尤其是在上个世纪70-80年代,曾经在一定的区域内进行过人为的广泛传播,对于收集、选择和建立基因库带来一定的难度。因此,急需解决判定种群起源的准确方法,为开展光皮梾木的育种提供必要的技术支持。
植物的基因组具有很好的稳定性,基本上不受环境影响,且取材方便。因此,通过对植株在基因组差异性的检测来追踪其起源是完全可行的。
dna分子标记是快速鉴定生物基因组差异的重要方法之一,其中微卫星标记具有多态性高、稳定性好、操作便捷等诸多优点,通过对目标植物种群进行微卫星标记的检测,不仅可以区分在性状上存在明显差异的个体,而且能够有效判别种群水平上的相似性。
目前国内外尚无对光皮梾木种群分子快速鉴定的相关报道。
技术实现要素:
为了克服上述现有技术的缺陷,本发明提供了一种非破坏性取样下快速鉴定光皮梾木种群的分子检测方法及其引物对,该鉴定方法准确、省时、省力。
为了实现上述发明目的,本发明采取了以下技术方案:
一种快速鉴定光皮梾木种群的分子检测方法,包括以下步骤:
(1)、以光皮梾木的dna为模板,分别以seqidno:1~2、seqidno:3~4、seqidno:5~6、seqidno:7~8、seqidno:9~10、seqidno:11~12、seqidno:13~14、seqidno:15~16、seqidno:17~18、seqidno:19~20、seqidno:21~22、seqidno:23~24、seqidno:25~26、seqidno:27~28、以及seqidno:29~30作为引物对,进行pcr扩增,获得微卫星分子标记数据;
(2)、对上述微卫星分子标记数据进行统计分析,鉴定归类光皮梾木种群。
在其中一些实施例中,步骤(1)中所述pcr扩增的反应程序为:
步骤s1,94℃下预变性5min;
步骤s2,94℃下变性30s;
步骤s3,57℃下退火30s;
步骤s4,72℃下延伸20s;
步骤s5,将所述步骤s2至所述步骤s4重复35次,且最后一次的所述步骤s4持续10min。
在其中一些实施例中,步骤(1)中所述pcr扩增的反应体系为:dna模板1.0μl、引物对0.2μl、mix10μl,加ddh2o至20μl。
本发明还提供了快速鉴定光皮梾木种群的引物对,采取了以下技术方案:
一种快速鉴定光皮梾木种群的引物对,所述引物对包括seqidno:1~2、seqidno:3~4、seqidno:5~6、seqidno:7~8、seqidno:9~10、seqidno:11~12、seqidno:13~14、seqidno:15~16、seqidno:17~18、seqidno:19~20、seqidno:21~22、seqidno:23~24、seqidno:25~26、seqidno:27~28、以及seqidno:29~30。
本发明通过对目标参试植株进行dna提取,根据光皮梾木15个稳定性好、多态性强的微卫星标记引物对进行dna扩增,获得分子标记数据后,采用统计分析软件对分子数据进行分析,从而对光皮梾木种群进行归类。与现有技术相比,本发明具有以下有益效果:
1、本发明的快速鉴定光皮梾木种群的分子检测方法在非破坏性取样的前提下快速获得基因组信息,工作量少且效率高,同时判别准确率高达95%,具有准确、省时和省力的优势;
2、本发明的快速鉴定光皮梾木种群的分子检测方法对于物种种群的快速分子检测具有重要价值和应用前景。
附图说明
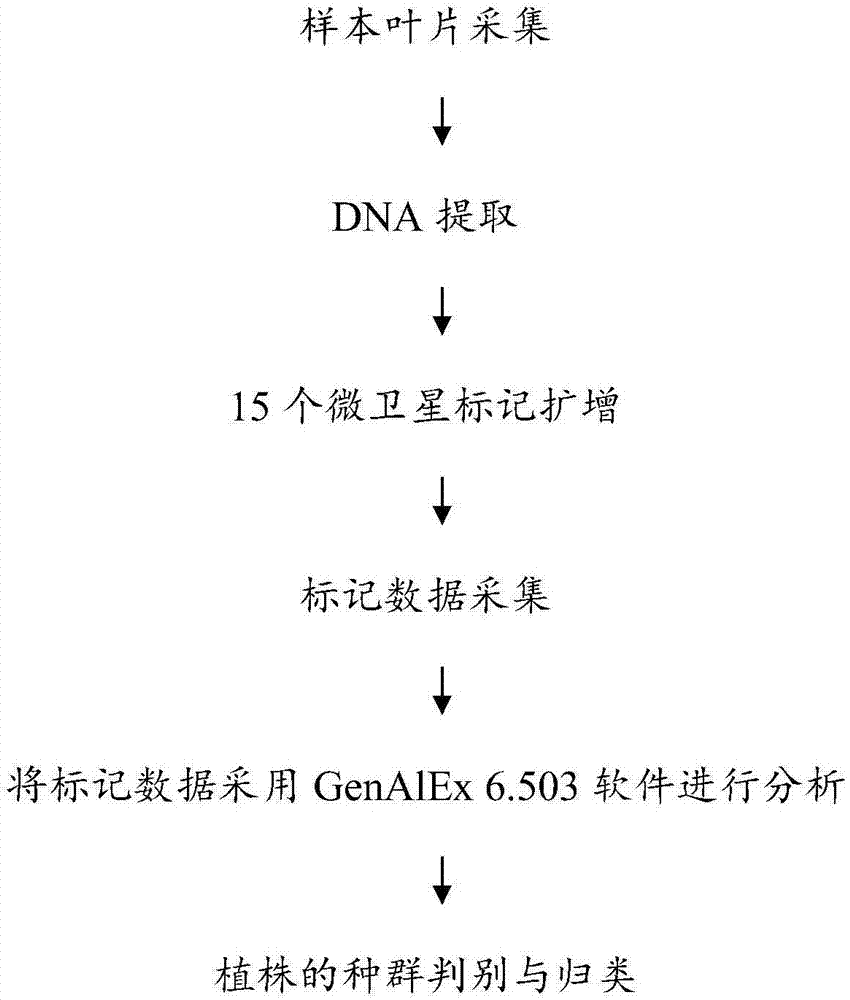
图1为本发明快速鉴定光皮梾木种群的分子检测方法的流程图;
图2为本发明实施例1中20个光皮梾木植株种群判别二维图,其中lc:广东乐昌种群;jx:江西赣州种群。
具体实施方式
下面结合附图和具体实施例进一步叙述本发明,本发明未述及之处适用于现有技术。下面给出本发明的具体实施例,但实施例仅是为了进一步详细叙述本发明,并不限制本发明的权利要求。
实施例1一种快速鉴定光皮梾木种群的分子检测方法
请参阅图1,为一种快速鉴定光皮梾木种群的分子检测方法的流程图,检测方法包括以下步骤:
(1)、按本领域常规方法对来自江西和广东2个种群共20个光皮梾木植株的叶片样品进行dna提取;
(2)、分别以步骤(1)提取的dna为模板,分别以seqidno:1~2、seqidno:3~4、seqidno:5~6、seqidno:7~8、seqidno:9~10、seqidno:11~12、seqidno:13~14、seqidno:15~16、seqidno:17~18、seqidno:19~20、seqidno:21~22、seqidno:23~24、seqidno:25~26、seqidno:27~28、以及seqidno:29~30作为引物对,分别进行pcr扩增,获得微卫星分子标记数据;
其中,引物对的序列如下:
每个pcr扩增的反应体系(20μl)为:
pcr扩增的反应程序为:
步骤s1,将所述全基因组dna依次在94℃下预变性5min;
步骤s2,将预变性产物在94℃下变性30s,得到变性产物;
步骤s3,将所述变性产物在57℃下退火30s,得到退火产物;
步骤s4,将所述退火产物在72℃下延伸20s;
步骤s5,将所述步骤s2至所述步骤s4重复35次,且最后一次的所述步骤s4持续10min。
(3)、统计分析鉴定归类光皮梾木种群。
采用非商业化genalex6.503软件对上述微卫星分子标记数据进行分析,统计分析的基本运算原理:根据同类性质的基因组信息(本实施例中为微卫星标记的dna片段大小)具有相似性的原理,也就是植株的相似度越高,标记的相似性就大,软件根据每个植株的微卫星标记的特征,计算出植株与植株之间在标记信息上的相似度,根据相似度的大小进行归类;得到植株的种群判别与归类。
江西和广东2个种群共20个植株叶片样品的统计分析结果如图2所示,结果表明,20个植株中7株来自广东种群,13株来自江西种群。
以上所述实施例的各技术特征可以进行任意的组合,为使描述简洁,未对上述实施例中的各个技术特征所有可能的组合都进行描述,然而,只要这些技术特征的组合不存在矛盾,都应当认为是本说明书记载的范围。
以上所述实施例仅表达了本发明的几种实施方式,其描述较为具体和详细,但并不能因此而理解为对发明专利范围的限制。应当指出的是,对于本领域的普通技术人员来说,在不脱离本发明构思的前提下,还可以做出若干变形和改进,这些都属于本发明的保护范围。因此,本发明专利的保护范围应以所附权利要求为准。
序列表
<110>广东省林业科学研究院
<120>快速鉴定光皮梾木种群的分子检测方法
<130>30
<170>patentinversion3.1
<210>1
<211>22
<212>dna
<213>人工序列
<400>1
catcgattaaggcagataagaa22
<210>2
<211>22
<212>dna
<213>人工序列
<400>2
tcaaatttcagagtctccacaa22
<210>3
<211>22
<212>dna
<213>人工序列
<400>3
gtggtggtgattaggaagctat22
<210>4
<211>22
<212>dna
<213>人工序列
<400>4
gtgacactggaatgaagagaga22
<210>5
<211>22
<212>dna
<213>人工序列
<400>5
aacgaaattgaaaccctagaaa22
<210>6
<211>22
<212>dna
<213>人工序列
<400>6
cagagacaaaattcaaaaagca22
<210>7
<211>22
<212>dna
<213>人工序列
<400>7
atggctatgatccaagttcttt22
<210>8
<211>22
<212>dna
<213>人工序列
<400>8
tcaaactgatcataaaacaggc22
<210>9
<211>22
<212>dna
<213>人工序列
<400>9
ggcggaagaactctatctttgt22
<210>10
<211>22
<212>dna
<213>人工序列
<400>19
tcagaacaacgtacgtacaaca22
<210>11
<211>22
<212>dna
<213>人工序列
<400>11
ggggtttatgttcttcagtagc22
<210>12
<211>22
<212>dna
<213>人工序列
<400>12
taccaccatcaatttctaaccc22
<210>13
<211>22
<212>dna
<213>人工序列
<400>13
tgtttcaagttaaggtcgattg22
<210>14
<211>22
<212>dna
<213>人工序列
<400>14
cttcaggtagaagtacccaagg22
<210>15
<211>22
<212>dna
<213>人工序列
<400>15
taaacaaaactgctgctgctat22
<210>16
<211>22
<212>dna
<213>人工序列
<400>16
agtccagaataaaaccactgct22
<210>17
<211>22
<212>dna
<213>人工序列
<400>17
caggctggtgtaactcataaaa22
<210>18
<211>22
<212>dna
<213>人工序列
<400>18
cactctcactacattgccctaa22
<210>19
<211>22
<212>dna
<213>人工序列
<400>19
agaagtattcctgtcctcatgc22
<210>20
<211>22
<212>dna
<213>人工序列
<400>20
aacccaagtaaacagaggaaac22
<210>21
<211>22
<212>dna
<213>人工序列
<400>21
ataatggctaacctacccaaga22
<210>22
<211>21
<212>dna
<213>人工序列
<400>22
cggtttgtaatagcactccac21
<210>23
<211>22
<212>dna
<213>人工序列
<400>23
ctgggacttcacacaagtagaa22
<210>24
<211>22
<212>dna
<213>人工序列
<400>24
aggtagagcattctggttccta22
<210>25
<211>21
<212>dna
<213>人工序列
<400>25
gatgatgacgattgattgagg21
<210>26
<211>22
<212>dna
<213>人工序列
<400>26
gttcagaaagaataccacccat22
<210>27
<211>23
<212>dna
<213>人工序列
<400>27
aatttgaaagaatacgtgattga23
<210>28
<211>22
<212>dna
<213>人工序列
<400>28
atgtcatttgactgtgggtaga22
<210>29
<211>22
<212>dna
<213>人工序列
<400>29
acaagcacgggcttatttatac22
<210>30
<211>22
<212>dna
<213>人工序列
<400>30
gttttcacagtgatcaaacgac22
- 还没有人留言评论。精彩留言会获得点赞!