一种靶向性抗肿瘤T细胞及其制备方法和应用与流程
本发明涉及医学生物领域,特别涉及一种靶向性抗肿瘤t细胞及其制备方法和应用。
背景技术:
肝细胞癌(hepatocellularcarcinoma,hcc)是世界范围内排位第五位的最常见的恶性肿瘤。在我国,每年由于肝癌死亡的人数超过十万。而嵌合抗原受体t细胞(chimericantigenreceptort-cell,car-t)作为当前最新的免疫细胞技术之一,因其治疗肿瘤具有特异性强、几乎无毒副作用的巨大优势而弥补了传统疗法的弊端,受到了广泛的关注和研究。它是将经过car改造的t细胞回输至人体,激活自身免疫系统,对肿瘤细胞进行杀伤,以达到清除恶性肿瘤细胞的目的,被认为最有可能彻底清除肿瘤细胞的方法。
但目前car-t技术的应用还局限于白血病、骨髓瘤、淋巴瘤等血液系统肿瘤,在诸如肝癌等实体肿瘤中的应用较少,且在复杂的肿瘤微环境中(如多种肿瘤抗原同时出现的情况),car-t细胞对肿瘤细胞的识别、杀伤能力大大降低,限制了其临床应用。
技术实现要素:
鉴于此,本发明提供了一种针对肝癌的靶向性抗肿瘤t细胞及其制备方法和应用。该t细胞可高效靶向至肝癌细胞的两个肿瘤靶点,对肝癌细胞的靶向性高、识别性较广且强,可避免肿瘤细胞出现靶点逃逸,具有较强的肝癌细胞杀伤性。
第一方面,本发明提供了一种靶向性抗肿瘤t细胞,所述靶向性抗肿瘤t细胞为带靶向cd133的嵌合抗原受体car-cd133和带靶向afp的嵌合抗原受体car-afp的双靶点嵌合抗原受体t细胞,或者为带所述car-cd133的嵌合抗原受体t细胞和带所述car-afp的嵌合抗原受体t细胞的混合,或者为带所述car-cd133的嵌合抗原受体t细胞和带所述car-afp的嵌合抗原受体t细胞的一种或多种与带所述car-cd133和所述car-afp的双靶点嵌合抗原受体t细胞的混合;其中,所述car-cd133包括从氨基端到羧基端顺次连接的靶向cd133的单链抗体、胞外铰链区、跨膜区和胞内信号区的氨基酸序列,所述car-afp包括从氨基端到羧基端顺次连接的靶向afp的单链抗体、胞外铰链区、跨膜区和胞内信号区的氨基酸序列;其中,所述靶向cd133的单链抗体的氨基酸序列包括如seqidno:1所示的氨基酸序列,所述靶向afp的单链抗体的氨基酸序列包括如seqidno:2所示的氨基酸序列。
其中,当所述靶向性抗肿瘤t细胞为带car-cd133和car-afp的双靶点car-t时,嵌合抗原受体car-cd133和car-afp的分布位置不作限定,可以是交替分布(例如abab…,aababb…)或依次分布(例如aaaa…bbb…),但两者之间并无共价连接,此时它们相应的cd133单链抗体和afp单链抗体之间也并无共价连接,这样可使它们保持较好的识别能力。
上述“从氨基端到羧基端顺次连接”具体为:所述靶向cd133的单链抗体或所述靶向afp的单链抗体的氨基酸序列的羧基端与所述胞外铰链区的氨基酸序列的氨基端相连,所述胞外铰链区的氨基酸序列的羧基端与所述跨膜区的氨基酸序列的氨基端相连,所述跨膜区的氨基酸序列的羧基端与所述胞内信号区的氨基酸序列的氨基端相连。
上述提及的cd133为5次跨膜糖蛋白,是公认的肿瘤干细胞标志物,在多种肿瘤组织中表达,可能与临床肝癌复发和转移有关,是较为常用的肝癌干细胞标志物。afp(甲胎蛋白)与肝癌及多种肿瘤的发生发展密切相关,目前临床上主要作为原发性肝癌的血清标志物。而本发明上述靶向性抗肿瘤t细胞带有car-cd133和car-afp,能同时识别两种不同的肝癌靶点cd133及afp,有效避免肝癌细胞出现免疫逃逸。
优选地,所述靶向性抗肿瘤t细胞为带car-cd133和带car-afp的双靶点嵌合抗原受体t细胞。这种情况下可降低在临床免疫治疗中所需要的t细胞数目。
可选地,所述靶向cd133的单链抗体的编码基因包括如seqidno:3所示的核苷酸序列,所述靶向afp的单链抗体的编码基因包括如seqidno:4所示的核苷酸序列。本发明所述靶向cd133的单链抗体保留有对cd133抗原的亲和活性,能够高效识别表面表达有cd133抗原的肿瘤细胞。类似地,所述靶向afp的单链抗体也保留有对afp抗原的亲和活性,能够高效识别表面表达有afp抗原的b系恶性淋巴细胞。
可选地,所述靶向cd133的单链抗体的氨基酸序列的编码基因应该考虑简并碱基,即如seqidno:1所示的氨基酸序列的编码基因包括如seqidno:3所示的核苷酸序列,保护范围还应该包括与seqidno:3具有碱基简并性质的核苷酸序列,这些核苷酸序列对应的氨基酸序列仍然为seqidno:1。所述靶向afp的单链抗体的氨基酸序列的编码基因同样应该考虑简并碱基。
本发明中,所述car-cd133中的胞外铰链区用于促进所述靶向cd133的单链抗体与肿瘤细胞上的cd133抗原结合;类似地,所述car-afp中的胞外铰链区用于促进所述靶向afp的单链抗体与肿瘤细胞上的afp结合。
可选地,所述胞外铰链区包括cd8α铰链区、cd28铰链区、cd4铰链区、cd5铰链区、cd134铰链区、cd137铰链区、icos铰链区中的一种或多种的组合。
进一步可选地,所述胞外铰链区为cd8α铰链区。可选地,所述cd8α铰链区的氨基酸序列包括如seqidno:9所示的氨基酸序列。可选地,所述cd8α铰链区的编码基因包括如seqidno:10所示的核苷酸序列。
可选地,所述cd8α铰链区的编码基因应该考虑简并碱基,即如seqidno:9所示的氨基酸序列的编码基因包括如seqidno:10所示的核苷酸序列,保护范围还应该保护与seqidno:10具有碱基简并性质的核苷酸序列,这些核苷酸序列对应的氨基酸序列仍然为seqidno:9。
本发明中,所述car-cd133中的跨膜区用于固定所述靶向cd133的嵌合抗原受体car-cd133;类似地,所述car-afp中的跨膜区用于固定所述靶向afp的嵌合抗原受体car-afp。
可选地,所述跨膜区包括cd3跨膜区、cd4跨膜区、cd8跨膜区、cd28跨膜区中的一种或多种的组合。
进一步可选地,所述跨膜区为cd8跨膜区。可选地,所述cd8跨膜区的氨基酸序列包括如seqidno:11所示的氨基酸序列。可选地,所述cd8跨膜区的编码基因包括如seqidno:12所示的核苷酸序列。
可选地,所述cd8跨膜区的编码基因应该考虑简并碱基,即如seqidno:11所示的氨基酸序列的编码基因还可包括与seqidno:12具有碱基简并性质的核苷酸序列。
本发明中,所述胞内信号区用于提供t细胞活化的信号,维持t细胞的生存时间和激活t细胞增殖信号通路。
可选地,所述胞内信号区包括4-1bb信号区、cd3ζ信号区、icos信号区、cd27信号区、ox40信号区、cd28信号区、il1r1信号区、cd70信号区、tnfrsf19l信号区中的一种或多种的组合。
在本发明一实施方式中,所述胞内信号区为从氨基端到羧基端顺次连接的4-1bb信号区和cd3ζ信号区。相应地,所述胞内信号区的编码基因包括从5’端到3’端顺次连接的4-1bb信号区的编码基因和cd3ζ信号区的编码基因。
其中,cd3ζ信号区为胞内信号传导结构域(第一信号区),4-1bb信号区为共刺激结构域,在它们的共同作用下,t细胞在识别抗原后被完全活化。进一步可选的,所述跨膜区的氨基酸序列的羧基端与所述4-1bb信号区的氨基酸序列的氨基端相连,所述4-1bb信号区的氨基酸序列的羧基端与所述cd3ζ信号区的氨基酸序列的氨基端相连。
可选地,所述4-1bb信号区的氨基酸序列包括如seqidno:13所示的氨基酸序列。可选地,所述4-1bb信号区的编码基因包括如seqidno:14所示的核苷酸序列。
可选地,所述4-1bb信号区的编码基因应该考虑简并碱基,即如seqidno:13所示的氨基酸序列的编码基因还应该包括与seqidno:14具有碱基简并性质的核苷酸序列。
可选地,所述cd3ζ信号区的氨基酸序列包括如seqidno:15所示的氨基酸序列。
可选地,所述cd3ζ信号区的编码基因包括如seqidno:16所示的核苷酸序列。
可选地,所述cd3ζ信号区的编码基因应该考虑简并碱基,即如seqidno:15所示的氨基酸序列的编码基因还应该包括与seqidno:16具有碱基简并性质的核苷酸序列。
需要说明的是,本发明中,所述car-cd133中的胞外铰链区、跨膜区和胞内信号区的氨基酸序列,与所述car-afp中对应的胞外铰链区、跨膜区和胞内信号区对应的氨基酸序列可以相同,也可以不同。
在本发明一实施方式中,所述car-cd133的氨基酸序列包括如seqidno:5所示的氨基酸序列。可选地,所述car-cd133的编码基因包括如seqidno:17所示的核苷酸序列。
可选地,所述car-cd133的编码基因应该考虑简并碱基,即如seqidno:5所示的氨基酸序列的编码基因还应该包括与seqidno:17具有碱基简并性质的核苷酸序列。
在本发明一实施方式中,所述car-afp的氨基酸序列包括如seqidno:6所示的氨基酸序列。可选地,所述car-afp的编码基因包括如seqidno:18所示的核苷酸序列。
可选地,所述car-afp的编码基因应该考虑简并碱基,即如seqidno:6所示的氨基酸序列的编码基因还应该包括与seqidno:18具有碱基简并性质的核苷酸序列。
本发明第一方面提供的靶向性抗肿瘤t细胞,包括靶向cd133的嵌合抗原受体car-cd133和靶向afp的嵌合抗原受体car-afp,能同时识别两种不同的肝癌靶点,增强了对肝癌细胞的识别,有效避免肝癌细胞出现免疫逃逸。具体地,当car-cd133和car-afp与肝癌细胞上相应的抗原蛋白结合后,所述靶向性抗肿瘤t细胞的胞内信号区被激活,促进t细胞在患者体内的扩增,高效且特异性地杀伤肿瘤细胞(具体可为表达cd133和/或afp的肝癌细胞),治疗效果较好。此外由于所述cd133和afp的单链抗体为人源化单链抗体,这使得该抗肿瘤t细胞避免引起人机体的免疫反应,具有持久的在体维持能力,如活性和杀伤力。
第二方面,本发明提供了一种重组病毒载体,包括如第一方面所述的靶向性抗肿瘤t细胞中所述car-cd133和/或car-afp的编码基因。
可选地,当所述重组病毒载体含有car-cd133的编码基因和car-afp的编码基因时,在所述重组病毒载体上所述car-cd133的编码基因和所述car-afp的编码基因之间,还包括一特殊序列,该特殊序列用于使所述car-cd133编码基因和所述car-afp的编码基因在转录翻译后可以得到两个独立的蛋白car-cd133和car-afp。在采用这样的重组病毒载体转染cd3阳性t淋巴细胞后,所得的靶向性抗肿瘤t细胞为带car-cd133和car-afp的双靶点嵌合抗原受体t细胞。进一步可选地,所述特殊序列可以是rbs序列、ires序列、t2a序列或其他蛋白酶序列等。
可选地,所述重组病毒载体带有所述car-cd133的编码基因,或者带有所述car-afp的编码基因。优选采用car-cd133编码基因的重组病毒载体与带car-afp编码基因的重组病毒载体分开或同时地共同感染t淋巴细胞,可得到如本发明第一方面所述的靶向性抗肿瘤t细胞,且所述重组病毒载体的感染效率较高,所得靶向性抗肿瘤t细胞能较充分地表达car-cd133和/或car-afp。
可选地,所述car-cd133的编码基因包括如seqidno:17所示的核苷酸序列。
优选地,所述car-cd133的编码基因包括如seqidno:19所示的核苷酸序列。如seqidno:19所示的核苷酸序列与如seqidno:17所示的核苷酸序列相比,多了下文所述的连接肽的编码基因。所述信号肽的编码基因可以较好地指导所述嵌合抗原受体car-cd133表达到细胞表面。
可选地,所述car-afp的编码基因包括如seqidno:18所示的核苷酸序列。
优选地,所述car-afp的编码基因包括如seqidno:20所示的核苷酸序列。seqidno:20所示的核苷酸序列与seqidno:18所示的核苷酸序列相比,多了下文所述的连接肽的编码基因。所述信号肽的编码基因可以较好地指导所述嵌合抗原受体car-afp达到细胞表面。
可选地,所述重组病毒载体中的病毒载体包括慢病毒载体、腺病毒载体或逆转录病毒载体。进一步可选地,所述病毒载体为慢病毒载体。在本发明第四方面提供的制备方法的步骤(1)-(3)示出了所述重组病毒载体的制备过程。
本发明第二方面提供的所述重组病毒载体具有较高的感染效率以及转录效率,其中的car-cd133和/或car-afp的编码基因片段能通过基因重组插入宿主基因组,得到上述靶向性抗肿瘤t细胞,使其持续、稳定地发挥靶向、杀伤效力。
第三方面,本发明提供了一种宿主细胞,包含如第二方面所述的重组慢病毒载体。
本发明第三方面提供的所述宿主细胞用于组装如第二方面所述的重组病毒载体,使其具有感染性。
可选地,所述宿主细胞包括但不限于hek293t细胞、293细胞、293t细胞、293ft细胞、sw480细胞、u87mg细胞、hos细胞、cos1细胞和cos7细胞。
第四方面,本发明提供了一种靶向性抗肿瘤t细胞的制备方法,包括:
(1)分别提供靶向cd133的嵌合抗原受体car-cd133的编码基因和靶向afp的嵌合抗原受体car-afp的编码基因;
所述car-cd133的编码基因包括从5’端到3’端顺次连接信号肽的编码基因、靶向cd133的单链抗体的编码基因、胞外铰链区的编码基因、跨膜区的编码基因和胞内信号区的编码基因;所述car-afp的编码基因包括从5’端到3’端顺次连接信号肽的编码基因、靶向afp的单链抗体的编码基因、胞外铰链区的编码基因、跨膜区的编码基因和胞内信号区的编码基因;
其中,所述靶向cd133的单链抗体的编码基因包括如seqidno:1所示的氨基酸序列所对应的核苷酸序列,所述靶向afp的单链抗体的编码基因包括如seqidno:2所示的氨基酸序列所对应的核苷酸序列;
(2)将所述car-cd133的编码基因和所述car-afp的编码基因分别插入到pwpxld载体中,得到pwpxld-car-cd133重组质粒和pwpxld-car-afp重组质粒;
(3)分别对所述pwpxld-car-cd133重组质粒和所述pwpxld-car-afp重组质粒进行包装,得到带car-cd133编码基因的第一重组慢病毒以及带car-afp编码基因的第二重组慢病毒;
(4)将所述第一重组慢病毒与所述第二重组慢病毒分开或同时地联合转染cd3阳性t淋巴细胞,经分离获得靶向性抗肿瘤t细胞。
以car-cd133的编码基因为例,上述“从5’端到3’端顺次连接”具体为:所述信号肽的编码基因的3’端与所述靶向cd133的单链抗体的编码基因的5’端相连,所述靶向cd133的单链抗体的编码基因的3’端与所述胞外铰链区编码基因的5’端相连,所述胞外铰链区的编码基因的3’端与所述跨膜区的编码基因的5’端相连,所述跨膜区的编码基因的3’端与所述胞内信号区的编码基因的5’端相连。
所述信号肽的编码基因用于指导所述嵌合抗原受体car-cd133或car-afp表达到细胞表面,其在蛋白翻译成熟过程中被信号肽酶切割。而car-cd133的编码基因中信号肽与所述car-afp的编码基因中信号肽的氨基酸序列可以相同,也可以不同,也可以是它们的信号肽的氨基酸序列相同,而核苷酸序列不同。
可选地,所述信号肽的氨基酸序列包括如seqidno:21所示的氨基酸序列。
可选地,所述信号肽的编码基因包括如seqidno:22所示的核苷酸序列。
可选地,所述信号肽的编码基因应该考虑简并碱基,即如seqidno:21所示的氨基酸序列的编码基因还应该包括与seqidno:22具有碱基简并性质的核苷酸序列。
对于所述胞外铰链区、跨膜区、胞内信号区的具体选择及相应的编码基因序列,可参见本发明第一方面所述,这里不再赘述。
可选地,所述car-cd133的编码基因包括如seqidno:7所示的氨基酸序列对应的核苷酸序列。
可选地,所述car-cd133的编码基因包括如seqidno:19所示的核苷酸序列。car-cd133的编码基因也可包括与seqidno:19的序列具有碱基简并性质的核苷酸序列。
可选地,所述car-afp的编码基因包括如seqidno:8所示的氨基酸序列对应的核苷酸序列。可选地,所述car-afp的编码基因包括如seqidno:20所示的核苷酸序列。所述car-afp的编码基因也可包括与seqidno:20所示序列具有碱基简并性质的核苷酸序列。
以car-cd133为例,seqidno:19与seqidno:17所示的核苷酸序列相比,多了连接肽的编码基因,但在嵌合抗原受体car-cd133表达到t细胞表面时,信号肽在蛋白翻译成熟过程中被信号肽酶切割。因此,在翻译成的嵌合抗原受体car-cd133的氨基酸序列(seqidno:5)中并未带有如seqidno:21所示的氨基酸序列。car-afp与之类似。
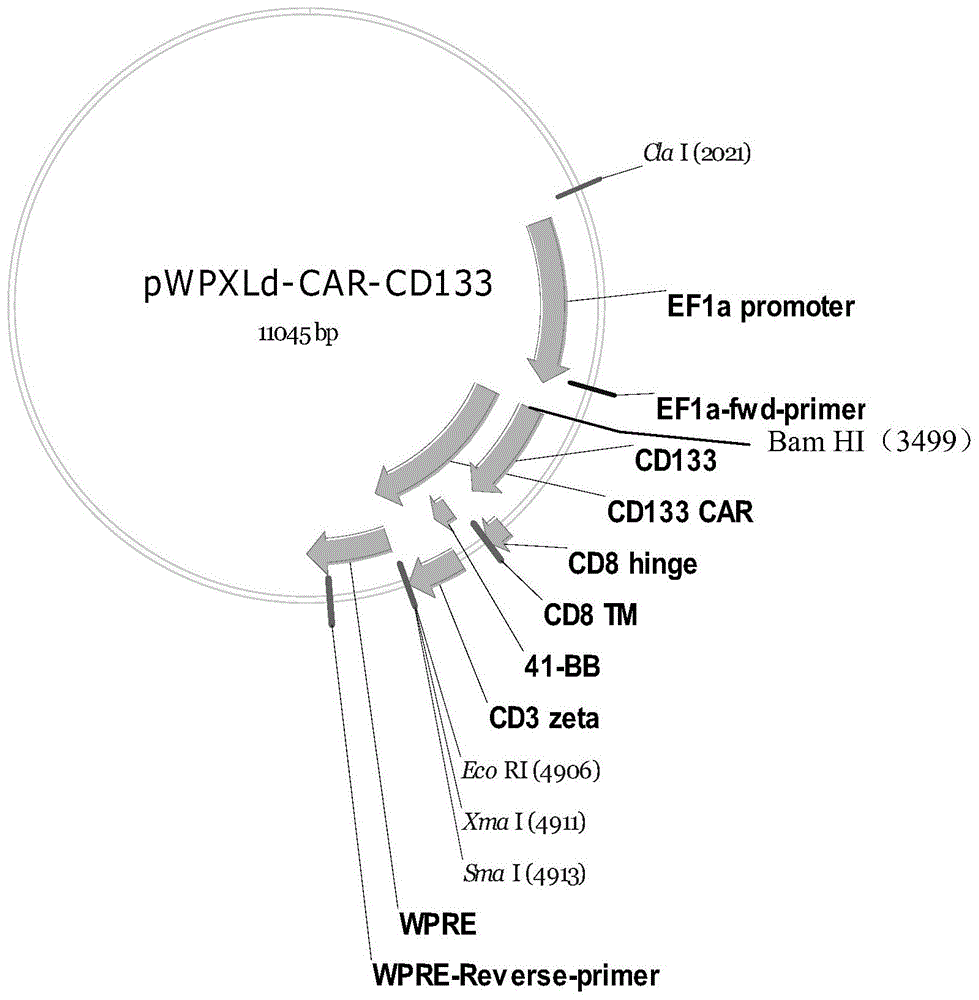
以car-cd133为例,所述car-cd133的编码基因序列插入到pwpxld载体中bamhⅰ和ecorⅰ酶切位点之间,且位于pwpxld载体的延伸因子1α(ef1α)之后,以ef1α为启动子。所述car-cd133的编码基因序列插入到pwpxld载体时,所述car-cd133的基因序列的5’端还可加入起始密码子(如atg)与pwpxld载体中bamh1酶切位点相连,3’端还可加入终止密码子与pwpxld载体中ecor1酶切位点相连。car-afp的情况与之相同。
可选地,步骤(3)中,所述“分别对所述pwpxld-car-cd133重组质粒和所述pwpxld-car-afp重组质粒进行包装,得到带car-cd133编码基因的第一重组慢病毒以及带car-afp编码基因的第二重组慢病毒”,包括:将所述pwpxld-car-cd133重组质粒与包膜质粒和包装质粒共转染宿主细胞,得到所述第一重组慢病毒;将所述pwpxld-car-afp重组质粒与包膜质粒和包装质粒共转染宿主细胞,得到所述第二重组慢病毒。
采用本发明所述的方式制备重组质粒及包装病毒,其中,所述pwpxld-car-cd133重组质粒和pwpxld-car-afp重组质粒上,car-cd133和car-afp的编码基因经过了密码子优化,且分子量适宜,重组慢病毒的包装效率高,同时通过宿主细胞制得的病毒的浓度较高。相应地,采用第一重组慢病毒和第二重组慢病毒来联合转染cd3阳性t淋巴细胞时,这两种重组慢病毒的用量较低,可降低实验成本。
本发明一实施方式中,所述包膜质粒为pmd2g,所述包装质粒为pspax2,所述宿主细胞为hek293t细胞。其中,所述包膜质粒pmd2g编码水疱性口炎病毒糖蛋白衣壳,所述水疱性口炎病毒糖蛋白衣壳可以协助重组慢病毒向细胞膜粘附,并保持重组慢病毒的感染性。
可选地,步骤(4)中,所述cd3阳性t淋巴细胞的获得过程如下:先将外周血单个核细胞按一定比例加入cd3/cd28免疫磁珠,并孵育一段时间后,放入磁铁进行筛选,得到免疫磁珠包被的cd3阳性t淋巴细胞,去除磁珠后,获得cd3阳性t淋巴细胞。
其中,步骤(4)中,将所述第一重组慢病毒和所述第二重组慢病毒分开或同时地联合转染cd3阳性t淋巴细胞,包括:先采用所述第一重组慢病毒转染cd3阳性t淋巴细胞后,再采用所述第二重组慢病毒进行转染;或先采用所述第二重组慢病毒转染cd3阳性t淋巴细胞后,再采用所述第一重组慢病毒进行转染;或采用所述第一重组慢病毒和所述第二重组慢病毒同时地转染cd3阳性t淋巴细胞。这里“联合转染”是指针对同一组细胞进行。
进一步地,步骤(4)中,第一重组慢病毒与第一重组慢病毒的病毒滴度之比是1:(0.5-2)。
本发明步骤(4)中所得到的靶向性抗肿瘤t细胞,如本发明第一方面所述。
此时,靶向性抗肿瘤t细胞的表面具有两个独立的、未共价结合的嵌合抗原受体(也即是有两个独立的单链抗体),不影响它们对各自靶标的识别、结合,能同时、高效地识别肝癌细胞上的cd133和afp靶标。所述靶向性抗肿瘤t细胞对表达cd133和afp中一种或两种的肿瘤细胞均能识别和杀伤,可避免肿瘤细胞出现靶点逃逸,提高了其靶向识别的广度和强度,以及杀伤广谱性,在复杂的肿瘤微环境下也具有较强的肿瘤杀伤能力。
在本发明另一实施方式中,当所需靶向性抗肿瘤t细胞为带所述car-cd133的嵌合抗原受体t细胞和带所述car-afp的嵌合抗原受体t细胞的混合时,也可以采用以下方式制得:采用上述第一重组慢病毒转染cd3阳性t淋巴细胞,得到带所述car-cd133的嵌合抗原受体t细胞;采用上述第二重组慢病毒转染cd3阳性t淋巴细胞,得到带所述car-afp的嵌合抗原受体t细胞;然后将这两种嵌合抗原受体t细胞进行混合。
本发明第四方面提供的靶向性抗肿瘤t细胞的制备方法中,采用带car-cd133编码基因的第一重组慢病毒以及带car-afp编码基因的第二重组慢病毒分别或同时地联合转染cd3阳性t淋巴细胞,可使得制得的靶向性抗肿瘤t细胞上嵌合抗原受体car-cd133和car-afp的表达效率更高,以具有较好的肿瘤识别、杀伤能力。
第五方面,本发明提供了一种如本发明第一方面所述的靶向性抗肿瘤t细胞、如本发明第二方面所述的重组病毒载体、如本发明第三方面所述的宿主细胞或如本发明第四方面所述的制备方法制得的靶向性抗肿瘤t细胞在制备诊断和/或治疗恶性肿瘤的药物中的应用。
特别地,适用于表达cd133和/或afp的恶性肿瘤(例如肝癌等)的诊断和治疗。可选地,在制备诊断和治疗肝癌的药物中的应用。
所述应用可以具体为:提供了一种试剂盒,所述试剂盒包括如第一方面所述的靶向性抗肿瘤t细胞或采用如第二方面所述的重组病毒载体转染得到的靶向性抗肿瘤t细胞或采用如第四方面所述的制备方法所制得的靶向性抗肿瘤t细胞,如本发明第二方面所述的重组病毒载体、如本发明第四方面所述的宿主细胞中的一种或多种。
附图说明
图1为本发明实施例提供的pwpxld-car-cd133重组质粒的质粒图谱。
图2为本发明实施例提供的pwpxld-car-afp重组质粒的质粒图谱。
图3为本发明实施例提供的靶向性抗肿瘤t细胞的体外肿瘤细胞杀伤效果图。
图4为本发明实施例提供的靶向性抗肿瘤t细胞治疗肿瘤小鼠的效果图。
具体实施方式
以下所述是本发明的优选实施方式,应当指出,对于本技术领域的普通技术人员来说,在不脱离本发明原理的前提下,还可以做出若干改进和润饰,这些改进和润饰也视为本发明的保护范围。
实施例一一种靶向性抗肿瘤t细胞的制备方法,包括以下步骤:
(1)制备靶向cd133的嵌合抗原受体car-cd133的基因
分别制备信号肽、靶向cd133的单链抗体、cd8α铰链区、cd8跨膜区、4-1bb信号区和cd3ζ信号区的编码基因;所述car-cd133中,信号肽的编码基因如seqidno:22所示,靶向cd133的单链抗体的编码基因如seqidno:3所示,cd8α铰链区的编码基因如seqidno:10所示,所述cd8跨膜区的编码基因如seqidno:12所示,所述4-1bb信号区的编码基因如seqidno:14所示,所述cd3ζ信号区的编码基因如seqidno:16所示。
通过pcr的方法将上述信号肽、靶向cd133的单链抗体、cd8α铰链区、cd8跨膜区、4-1bb信号区和cd3ζ信号区的编码基因依次从5’端到3’端连接到一起,得到car-cd133的编码基因,该car-cd133的编码基因如seqidno:19所示。
(2)制备靶向afp的嵌合抗原受体car-afp的基因
分别制备信号肽、靶向afp的单链抗体、cd8α铰链区、cd8跨膜区、4-1bb信号区和cd3ζ信号区的编码基因;其中,靶向afp的单链抗体的编码基因如seqidno:4所示,其他区段的编码基因如上所述。
通过pcr的方法将上述信号肽、靶向afp的单链抗体、cd8α铰链区、cd8跨膜区、4-1bb信号区和cd3ζ信号区的编码基因依次从5’端到3’端连接到一起,得到car-afp的编码基因,该car-afp的编码基因如seqidno:20所示。
(3)构建pwpxld-car-cd133重组质粒和pwpxld-car-afp重组质粒
将car-cd133的编码基因插入到pwpxld载体的bamhⅰ和ecorⅰ酶切位点之间,并在pwpxld载体ef1α之后,以ef1α为启动子(当所述car-cd133的编码基因插入到pwpxld载体时,所述car-cd133的编码基因的5’端可加入起始密码子(如atg)与pwpxld载体中bamhⅰ酶切位点相连,3’端可加入终止密码子(如taa)与pwpxld载体中ecorⅰ酶切位点相连)。然后将其转入大肠杆菌感受态细胞dh5α,进行阳性克隆pcr鉴定和测序鉴定。经过pcr产物凝胶电泳检测和测序鉴定符合目的片段大小和序列,成功构建如图1所示的pwpxld-car-cd133重组质粒,并将该重组质粒放置于-80℃下保存。
按与上述类似的方法,将car-afp的编码基因构建成如图2所示的pwpxld-car-afp重组质粒,并将该重组质粒放置于-80℃下保存。
(4)重组慢病毒构建
将pwpxld-car-afp重组质粒、包装质粒pspax2、包膜质粒pmd2g三者共转染培养好的hek293t细胞。第48h收获含病毒的上清,经0.45μm滤膜过滤,-80℃超低温冰箱中保存;第72h二次收获含病毒的上清,0.45μm滤膜过滤,与第48h收获的病毒上清合并在一起加入超速离心管中,逐一放入至beckman超速离心机内,设置离心参数为25000rpm,离心时间为2h,离心温度控制在4℃;离心结束后,弃去上清,尽量去除残留在管壁上的液体,加入病毒保存液,轻轻反复吹打重悬;经充分溶解后,高速离心10000rpm,离心5min后,取上清采用荧光法测定滴度,将病毒按照100μl、2×108tu/ml分装,保存于-80℃的超低温冰箱,得到带car-cd133的第一重组慢病毒。
按与上述类似的方法,将pwpxld-car-afp重组质粒与包装质粒pspax2、包膜质粒pmd2g三者共转染入培养好的hek293t细胞,组装得到带car-afp的第二重组慢病毒。
(5)靶向性抗肿瘤t细胞的制备
a)pbmc(外周血单个核细胞)的分离
pbmc来源于自体静脉血、自体骨髓、脐带血和胎盘血等。最好是来源于癌症患者手术一个月后、放化疗一个月后采集的新鲜外周血或骨髓。抽取病人血液,送样至血液分离室;采集外周血单个核细胞,ficoll离心分离后取中间层细胞;经pbs洗涤后,得到pbmc。
b)免疫磁珠法分离抗原特异性t淋巴细胞
取上述pbmc,加入不含血清的x-vivo15基础培养基(lonza公司,货号:04-744q),配成细胞悬液;按磁珠与细胞的比例为3:1,加入cd3/cd28免疫磁珠(
c)病毒转染法制备靶向性抗肿瘤t淋巴细胞
取上述经过免疫磁珠分离法得到的cd3阳性t淋巴细胞,同时加入与cd3阳性细胞数相应的病毒滴度的带car-cd133的第一重组慢病毒和带car-afp的第二重组慢病毒进行共同培养,其中第一重组慢病毒与第二重组慢病毒的用量(滴度)之比是1:1。
培养的第3天,进行细胞计数和换液,调整细胞浓度为1×106个/ml,接种,培养;培养的第5天,观察细胞状态,如果细胞密度增大,则稀释细胞浓度为1×106个/ml,检测细胞活性,继续培养。扩增培养到第9-11天,收集细胞,得到靶向性抗肿瘤t细胞,然后将其保存在回输专用的细胞冻存液中。
实施例二一种靶向性抗肿瘤t细胞的制备方法,包括:
按照实施例一中的方法制备得到带car-cd133的第一重组慢病毒和带car-afp的第二重组慢病毒,将带car-cd133的第一重组慢病毒转染cd3阳性t淋巴细胞,按照实施例一中相同的培养条件和时间进行培养,经过收集得到靶向cd133的嵌合抗原受体t细胞。再将带car-afp的第二重组慢病毒转染所述靶向cd133的嵌合抗原受体t细胞,培养到第9-11天,收集细胞,得到所述靶向性抗肿瘤t细胞,然后将其保存在回输专用的细胞冻存液中。
实施例三一种靶向性抗肿瘤t细胞的制备方法,包括:
按照实施例一中的方法制备得到带car-cd133的第一重组慢病毒和带car-afp的第二重组慢病毒。先将带car-afp的第二重组慢病毒转染cd3阳性t淋巴细胞,按照实施例一中相同的培养条件和时间进行培养,经过收集得到靶向afp的嵌合抗原受体t细胞;再将带car-cd133的第一重组慢病毒转染所述靶向afp的嵌合抗原受体t细胞,培养到第9-11天,收集细胞,得到靶向性抗肿瘤t细胞,然后将其保存在回输专用的细胞冻存液中。
效果实施例
效果实施例一:评估本发明靶向性抗肿瘤t细胞的体外肿瘤细胞杀伤情况
将本发明实施例一制得的靶向性抗肿瘤t细胞(实验组,这里具体选用带car-cd133和car-afp的双靶点嵌合抗原受体t细胞)与未经制备的t淋巴细胞(阴性对照组)、具有单独的car-cd133的t细胞(cd133car-t单独组)以及具有单独的car-afp的t细胞(afpcar-t单独组)进行比较,在体外将上述四组效应细胞与靶细胞(hepg2细胞)按数量比为1:10、1:3、1:1、3:1和10:1的比例,在37℃、5%co2下进行共培养,在培养后的第15-18小时,收集细胞,进行流式染色,检测细胞杀伤情况,结果如图3所示。从图3中可看出,相较于对照组,经本发明方法制备的靶向性抗肿瘤t细胞具有超强的肿瘤杀伤能力。
效果实施例二:评估本发明靶向性抗肿瘤t细胞对小鼠体内肿瘤细胞杀伤情况
将本发明实施例一制得的靶向性抗肿瘤t细胞(实验组,这里具体选用带car-cd133和car-afp的双靶点嵌合抗原受体t细胞)与未经制备的t淋巴细胞(阴性对照组)、具有单独的car-cd133的t细胞(cd133car-t单独组)以及具有单独的car-afp的t细胞(afpcar-t单独组),在小鼠肝癌模型中,给每只小鼠尾静脉注射1×106个t细胞(n=9),得到小鼠的生存曲线,结果如图4所示。从图4可以看出,本发明提供的靶向性抗肿瘤t细胞在注入小鼠体内40天后,仍能使小鼠的存活率稳定在52%左右,远远超过阴性对照组和以上两个单独组。这表明本发明提供的靶向性抗肿瘤t细胞能够更好地保护小鼠免于因肝癌导致的死亡。
序列表
<110>深圳市第三人民医院
<120>一种靶向性抗肿瘤t细胞及其制备方法和应用
<160>22
<170>siposequencelisting1.0
<210>1
<211>243
<212>prt
<213>人工序列(artificialsequence)
<400>1
alaarghiscysserleuprovalserserasnhisvalcysileser
151015
argglygluglyhishisileleuglncysglnleulyscyslysleu
202530
tyrvalleuvalproalagluglnglyserserprolysprotrpile
354045
tyrargthrserasnleualaserglyvalproalaargphesergly
505560
serglyserglythrsertyrserleuthrilesersermetgluala
65707580
gluaspalaalathrtyrtyrcysglnglntyrhissertyrpropro
859095
thrpheglyalaglythrlysleugluleulysserserglyglygly
100105110
glyserglyglyglyglyglyglyserserargserserleugluval
115120125
lysleuvalgluserglyprogluleulyslysproglygluthrval
130135140
lysilesercyslysalaserglytyrthrphethrasptyrsermet
145150155160
histrpvalasnglnalaproglylysglyleulystrpmetglytrp
165170175
ileasnthrgluthrglygluprosertyralaaspaspphelysgly
180185190
argphealapheserleugluthrseralaserthralatyrleugln
195200205
ileasnasnleulysasngluaspthralathrtyrphecysalathr
210215220
asptyrglyasptyrpheasptyrtrpglyglnglythrthrleuthr
225230235240
valserser
<210>2
<211>237
<212>prt
<213>人工序列(artificialsequence)
<400>2
glnservalleuthrglnproalaservalserglyserproglygln
151015
serilethrilesercysthrglythrserseraspvalglyglytyr
202530
asntyrvalsertrptyrglnglnhisproglylysalaprolysleu
354045
metiletyraspvalasnasnargprosergluvalserasnargphe
505560
serglyserlysserglyasnthralaserleuthrileserglyleu
65707580
glnalagluaspglualaasptyrtyrcyssersertyrthrthrgly
859095
serargalavalpheglyglyglythrlysleuthrvalleuglygly
100105110
glyglyglyserglyglyglyglyserserglyglyglyserglnser
115120125
valleuthrglnproalaservalserglyserproglyglnserile
130135140
thrilesercysthrglythrserseraspvalglyglytyrasntyr
145150155160
valsertrptyrglnglnhisproglylysalaprolysleumetile
165170175
tyraspvalasnasnargprosergluvalserasnargphesergly
180185190
serlysserglyasnthralaserleuthrileserglyleuglnala
195200205
gluaspglualaasptyrtyrcyssersertyrthrthrglyserarg
210215220
alavalpheglyglyglythrlysleuthrvalleugly
225230235
<210>3
<211>729
<212>dna
<213>人工序列(artificialsequence)
<400>3
gctcgacattgttctctcccagtctccagcaatcatgtctgcatctccaggggagaaggt60
caccatatcctgcagtgccagctcaagtgtaagttatatgtactggtaccagcagaacaa120
ggatcctcccccaaaccctggatttatcgcacatccaacctggcttctggagtccctgct180
cgcttcagtggcagtgggtctgggacctcttactctctcacaatcagcagcatggaggct240
gaagatgctgccacttattactgccagcagtatcatagttacccacccacgttcggtgct300
gggaccaagctggagctgaaatcctctggtggcggtggctcgggcggtggtgggggtggt360
tcctctagatcttccctcgaggtgaagctggtggagtctggacctgagctgaagaagcct420
ggagagacagtcaagatctcctgcaaggcttctggttataccttcacagactattcaatg480
cactgggtgaatcaggctccaggaaagggtttaaagtggatgggctggataaacactgag540
actggtgagccatcatatgcagatgacttcaagggacggtttgccttctctttggaaacc600
tctgccagcactgcctatttgcagatcaacaacctcaaaaatgaggacacggctacatat660
ttctgtgctaccgattacggggactactttgactactggggccaaggcaccactctcaca720
gtctcctca729
<210>4
<211>711
<212>dna
<213>人工序列(artificialsequence)
<400>4
cagagcgtgctgacacagcctgcctccgtgtctggctctcctggccagtccatcaccatc60
agctgtaccggcaccagctccgacgtgggcggctacaattacgtgtcctggtatcagcag120
catcccggcaaggcccccaagctgatgatctacgacgtgaacaaccggcccagcgaggtg180
tccaacagattcagcggcagcaagagcggcaacaccgccagcctgacaatcagcggactg240
caggccgaggacgaggccgactactactgcagcagctacaccaccggcagcagagccgtg300
tttggcggaggcaccaagctgacagtgctgggcggaggcggaggatctggcggcggagga360
agttctggcggagggtctcagagcgtgctgacacagcctgcctccgtgtctggctctcct420
ggccagtccatcaccatcagctgtaccggcaccagctccgacgtgggcggctacaattac480
gtgtcctggtatcagcagcatcccggcaaggcccccaagctgatgatctacgacgtgaac540
aaccggcccagcgaggtgtccaacagattcagcggcagcaagagcggcaacaccgccagc600
ctgacaatcagcggactgcaggccgaggacgaggccgactactactgcagcagctacacc660
accggcagcagagccgtgtttggcggaggcaccaagctgacagtgctgggc711
<210>5
<211>466
<212>prt
<213>人工序列(artificialsequence)
<400>5
alaarghiscysserleuprovalserserasnhisvalcysileser
151015
argglygluglyhishisileleuglncysglnleulyscyslysleu
202530
tyrvalleuvalproalagluglnglyserserprolysprotrpile
354045
tyrargthrserasnleualaserglyvalproalaargphesergly
505560
serglyserglythrsertyrserleuthrilesersermetgluala
65707580
gluaspalaalathrtyrtyrcysglnglntyrhissertyrpropro
859095
thrpheglyalaglythrlysleugluleulysserserglyglygly
100105110
glyserglyglyglyglyglyglyserserargserserleugluval
115120125
lysleuvalgluserglyprogluleulyslysproglygluthrval
130135140
lysilesercyslysalaserglytyrthrphethrasptyrsermet
145150155160
histrpvalasnglnalaproglylysglyleulystrpmetglytrp
165170175
ileasnthrgluthrglygluprosertyralaaspaspphelysgly
180185190
argphealapheserleugluthrseralaserthralatyrleugln
195200205
ileasnasnleulysasngluaspthralathrtyrphecysalathr
210215220
asptyrglyasptyrpheasptyrtrpglyglnglythrthrleuthr
225230235240
valserserthrthrthrproalaproargproprothrproalapro
245250255
thrilealaserglnproleuserleuargproglualacysargpro
260265270
alaalaglyglyalavalhisthrargglyleuaspphealacysasp
275280285
iletyriletrpalaproleualaglythrcysglyvalleuleuleu
290295300
serleuvalilethrleutyrcyslysargglyarglyslysleuleu
305310315320
tyrilephelysglnprophemetargprovalglnthrthrglnglu
325330335
gluaspglycyssercysargpheproglugluglugluglyglycys
340345350
gluleuargvallyspheserargseralaaspalaproalatyrlys
355360365
glnglyglnasnglnleutyrasngluleuasnleuglyargargglu
370375380
glutyraspvalleuasplysargargglyargaspproglumetgly
385390395400
glylysproargarglysasnproglngluglyleutyrasngluleu
405410415
glnlysasplysmetalaglualatyrsergluileglymetlysgly
420425430
gluargargargglylysglyhisaspglyleutyrglnglyleuser
435440445
thralathrlysaspthrtyraspalaleuhismetglnalaleupro
450455460
proarg
465
<210>6
<211>460
<212>prt
<213>人工序列(artificialsequence)
<400>6
glnservalleuthrglnproalaservalserglyserproglygln
151015
serilethrilesercysthrglythrserseraspvalglyglytyr
202530
asntyrvalsertrptyrglnglnhisproglylysalaprolysleu
354045
metiletyraspvalasnasnargprosergluvalserasnargphe
505560
serglyserlysserglyasnthralaserleuthrileserglyleu
65707580
glnalagluaspglualaasptyrtyrcyssersertyrthrthrgly
859095
serargalavalpheglyglyglythrlysleuthrvalleuglygly
100105110
glyglyglyserglyglyglyglyserserglyglyglyserglnser
115120125
valleuthrglnproalaservalserglyserproglyglnserile
130135140
thrilesercysthrglythrserseraspvalglyglytyrasntyr
145150155160
valsertrptyrglnglnhisproglylysalaprolysleumetile
165170175
tyraspvalasnasnargprosergluvalserasnargphesergly
180185190
serlysserglyasnthralaserleuthrileserglyleuglnala
195200205
gluaspglualaasptyrtyrcyssersertyrthrthrglyserarg
210215220
alavalpheglyglyglythrlysleuthrvalleuglythrthrthr
225230235240
proalaproargproprothrproalaprothrilealaserglnpro
245250255
leuserleuargproglualacysargproalaalaglyglyalaval
260265270
histhrargglyleuaspphealacysaspiletyriletrpalapro
275280285
leualaglythrcysglyvalleuleuleuserleuvalilethrleu
290295300
tyrcyslysargglyarglyslysleuleutyrilephelysglnpro
305310315320
phemetargprovalglnthrthrglnglugluaspglycyssercys
325330335
argpheproglugluglugluglyglycysgluleuargvallysphe
340345350
serargseralaaspalaproalatyrlysglnglyglnasnglnleu
355360365
tyrasngluleuasnleuglyargarggluglutyraspvalleuasp
370375380
lysargargglyargaspproglumetglyglylysproargarglys
385390395400
asnproglngluglyleutyrasngluleuglnlysasplysmetala
405410415
glualatyrsergluileglymetlysglygluargargargglylys
420425430
glyhisaspglyleutyrglnglyleuserthralathrlysaspthr
435440445
tyraspalaleuhismetglnalaleuproproarg
450455460
<210>7
<211>486
<212>prt
<213>人工序列(artificialsequence)
<400>7
alaleuprovalthralaleuleuleuproleualaleuleuleuhis
151015
alaalaargproalaarghiscysserleuprovalserserasnhis
202530
valcysileserargglygluglyhishisileleuglncysglnleu
354045
lyscyslysleutyrvalleuvalproalagluglnglyserserpro
505560
lysprotrpiletyrargthrserasnleualaserglyvalproala
65707580
argpheserglyserglyserglythrsertyrserleuthrileser
859095
sermetglualagluaspalaalathrtyrtyrcysglnglntyrhis
100105110
sertyrproprothrpheglyalaglythrlysleugluleulysser
115120125
serglyglyglyglyserglyglyglyglyglyglyserserargser
130135140
serleugluvallysleuvalgluserglyprogluleulyslyspro
145150155160
glygluthrvallysilesercyslysalaserglytyrthrphethr
165170175
asptyrsermethistrpvalasnglnalaproglylysglyleulys
180185190
trpmetglytrpileasnthrgluthrglygluprosertyralaasp
195200205
aspphelysglyargphealapheserleugluthrseralaserthr
210215220
alatyrleuglnileasnasnleulysasngluaspthralathrtyr
225230235240
phecysalathrasptyrglyasptyrpheasptyrtrpglyglngly
245250255
thrthrleuthrvalserserthrthrthrproalaproargpropro
260265270
thrproalaprothrilealaserglnproleuserleuargproglu
275280285
alacysargproalaalaglyglyalavalhisthrargglyleuasp
290295300
phealacysaspiletyriletrpalaproleualaglythrcysgly
305310315320
valleuleuleuserleuvalilethrleutyrcyslysargglyarg
325330335
lyslysleuleutyrilephelysglnprophemetargprovalgln
340345350
thrthrglnglugluaspglycyssercysargpheproglugluglu
355360365
gluglyglycysgluleuargvallyspheserargseralaaspala
370375380
proalatyrlysglnglyglnasnglnleutyrasngluleuasnleu
385390395400
glyargarggluglutyraspvalleuasplysargargglyargasp
405410415
proglumetglyglylysproargarglysasnproglngluglyleu
420425430
tyrasngluleuglnlysasplysmetalaglualatyrsergluile
435440445
glymetlysglygluargargargglylysglyhisaspglyleutyr
450455460
glnglyleuserthralathrlysaspthrtyraspalaleuhismet
465470475480
glnalaleuproproarg
485
<210>8
<211>480
<212>prt
<213>人工序列(artificialsequence)
<400>8
alaleuprovalthralaleuleuleuproleualaleuleuleuhis
151015
alaalaargproglnservalleuthrglnproalaservalsergly
202530
serproglyglnserilethrilesercysthrglythrserserasp
354045
valglyglytyrasntyrvalsertrptyrglnglnhisproglylys
505560
alaprolysleumetiletyraspvalasnasnargprosergluval
65707580
serasnargpheserglyserlysserglyasnthralaserleuthr
859095
ileserglyleuglnalagluaspglualaasptyrtyrcysserser
100105110
tyrthrthrglyserargalavalpheglyglyglythrlysleuthr
115120125
valleuglyglyglyglyglyserglyglyglyglyserserglygly
130135140
glyserglnservalleuthrglnproalaservalserglyserpro
145150155160
glyglnserilethrilesercysthrglythrserseraspvalgly
165170175
glytyrasntyrvalsertrptyrglnglnhisproglylysalapro
180185190
lysleumetiletyraspvalasnasnargprosergluvalserasn
195200205
argpheserglyserlysserglyasnthralaserleuthrileser
210215220
glyleuglnalagluaspglualaasptyrtyrcyssersertyrthr
225230235240
thrglyserargalavalpheglyglyglythrlysleuthrvalleu
245250255
glythrthrthrproalaproargproprothrproalaprothrile
260265270
alaserglnproleuserleuargproglualacysargproalaala
275280285
glyglyalavalhisthrargglyleuaspphealacysaspiletyr
290295300
iletrpalaproleualaglythrcysglyvalleuleuleuserleu
305310315320
valilethrleutyrcyslysargglyarglyslysleuleutyrile
325330335
phelysglnprophemetargprovalglnthrthrglnglugluasp
340345350
glycyssercysargpheproglugluglugluglyglycysgluleu
355360365
argvallyspheserargseralaaspalaproalatyrlysglngly
370375380
glnasnglnleutyrasngluleuasnleuglyargarggluglutyr
385390395400
aspvalleuasplysargargglyargaspproglumetglyglylys
405410415
proargarglysasnproglngluglyleutyrasngluleuglnlys
420425430
asplysmetalaglualatyrsergluileglymetlysglygluarg
435440445
argargglylysglyhisaspglyleutyrglnglyleuserthrala
450455460
thrlysaspthrtyraspalaleuhismetglnalaleuproproarg
465470475480
<210>9
<211>45
<212>prt
<213>人工序列(artificialsequence)
<400>9
thrthrthrproalaproargproprothrproalaprothrileala
151015
serglnproleuserleuargproglualacysargproalaalagly
202530
glyalavalhisthrargglyleuaspphealacysasp
354045
<210>10
<211>135
<212>dna
<213>人工序列(artificialsequence)
<400>10
accacgacgccagcgccgcgaccaccaacaccggcgcccaccatcgcgtcgcagcccctg60
tccctgcgcccagaggcgtgccggccagcggcggggggcgcagtgcacacgagggggctg120
gacttcgcctgtgat135
<210>11
<211>24
<212>prt
<213>人工序列(artificialsequence)
<400>11
iletyriletrpalaproleualaglythrcysglyvalleuleuleu
151015
serleuvalilethrleutyrcys
20
<210>12
<211>72
<212>dna
<213>人工序列(artificialsequence)
<400>12
atctacatctgggcgcccttggccgggacttgtggggtccttctcctgtcactggttatc60
accctttactgc72
<210>13
<211>42
<212>prt
<213>人工序列(artificialsequence)
<400>13
lysargglyarglyslysleuleutyrilephelysglnprophemet
151015
argprovalglnthrthrglnglugluaspglycyssercysargphe
202530
proglugluglugluglyglycysgluleu
3540
<210>14
<211>126
<212>dna
<213>人工序列(artificialsequence)
<400>14
aaacggggcagaaagaaactcctgtatatattcaaacaaccatttatgagaccagtacaa60
actactcaagaggaagatggctgtagctgccgatttccagaagaagaagaaggaggatgt120
gaactg126
<210>15
<211>112
<212>prt
<213>人工序列(artificialsequence)
<400>15
argvallyspheserargseralaaspalaproalatyrlysglngly
151015
glnasnglnleutyrasngluleuasnleuglyargarggluglutyr
202530
aspvalleuasplysargargglyargaspproglumetglyglylys
354045
proargarglysasnproglngluglyleutyrasngluleuglnlys
505560
asplysmetalaglualatyrsergluileglymetlysglygluarg
65707580
argargglylysglyhisaspglyleutyrglnglyleuserthrala
859095
thrlysaspthrtyraspalaleuhismetglnalaleuproproarg
100105110
<210>16
<211>336
<212>dna
<213>人工序列(artificialsequence)
<400>16
agagtgaagttcagcaggagcgcagacgcccccgcgtacaagcagggccagaaccagctc60
tataacgagctcaatctaggacgaagagaggagtacgatgttttggacaagagacgtggc120
cgggaccctgagatggggggaaagccgagaaggaagaaccctcaggaaggcctgtacaat180
gaactgcagaaagataagatggcggaggcctacagtgagattgggatgaaaggcgagcgc240
cggaggggcaaggggcacgatggcctttaccagggtctcagtacagccaccaaggacacc300
tacgacgcccttcacatgcaggccctgccccctcgc336
<210>17
<211>1398
<212>dna
<213>人工序列(artificialsequence)
<400>17
gctcgacattgttctctcccagtctccagcaatcatgtctgcatctccaggggagaaggt60
caccatatcctgcagtgccagctcaagtgtaagttatatgtactggtaccagcagaacaa120
ggatcctcccccaaaccctggatttatcgcacatccaacctggcttctggagtccctgct180
cgcttcagtggcagtgggtctgggacctcttactctctcacaatcagcagcatggaggct240
gaagatgctgccacttattactgccagcagtatcatagttacccacccacgttcggtgct300
gggaccaagctggagctgaaatcctctggtggcggtggctcgggcggtggtgggggtggt360
tcctctagatcttccctcgaggtgaagctggtggagtctggacctgagctgaagaagcct420
ggagagacagtcaagatctcctgcaaggcttctggttataccttcacagactattcaatg480
cactgggtgaatcaggctccaggaaagggtttaaagtggatgggctggataaacactgag540
actggtgagccatcatatgcagatgacttcaagggacggtttgccttctctttggaaacc600
tctgccagcactgcctatttgcagatcaacaacctcaaaaatgaggacacggctacatat660
ttctgtgctaccgattacggggactactttgactactggggccaaggcaccactctcaca720
gtctcctcaaccacgacgccagcgccgcgaccaccaacaccggcgcccaccatcgcgtcg780
cagcccctgtccctgcgcccagaggcgtgccggccagcggcggggggcgcagtgcacacg840
agggggctggacttcgcctgtgatatctacatctgggcgcccttggccgggacttgtggg900
gtccttctcctgtcactggttatcaccctttactgcaaacggggcagaaagaaactcctg960
tatatattcaaacaaccatttatgagaccagtacaaactactcaagaggaagatggctgt1020
agctgccgatttccagaagaagaagaaggaggatgtgaactgagagtgaagttcagcagg1080
agcgcagacgcccccgcgtacaagcagggccagaaccagctctataacgagctcaatcta1140
ggacgaagagaggagtacgatgttttggacaagagacgtggccgggaccctgagatgggg1200
ggaaagccgagaaggaagaaccctcaggaaggcctgtacaatgaactgcagaaagataag1260
atggcggaggcctacagtgagattgggatgaaaggcgagcgccggaggggcaaggggcac1320
gatggcctttaccagggtctcagtacagccaccaaggacacctacgacgcccttcacatg1380
caggccctgccccctcgc1398
<210>18
<211>1380
<212>dna
<213>人工序列(artificialsequence)
<400>18
cagagcgtgctgacacagcctgcctccgtgtctggctctcctggccagtccatcaccatc60
agctgtaccggcaccagctccgacgtgggcggctacaattacgtgtcctggtatcagcag120
catcccggcaaggcccccaagctgatgatctacgacgtgaacaaccggcccagcgaggtg180
tccaacagattcagcggcagcaagagcggcaacaccgccagcctgacaatcagcggactg240
caggccgaggacgaggccgactactactgcagcagctacaccaccggcagcagagccgtg300
tttggcggaggcaccaagctgacagtgctgggcggaggcggaggatctggcggcggagga360
agttctggcggagggtctcagagcgtgctgacacagcctgcctccgtgtctggctctcct420
ggccagtccatcaccatcagctgtaccggcaccagctccgacgtgggcggctacaattac480
gtgtcctggtatcagcagcatcccggcaaggcccccaagctgatgatctacgacgtgaac540
aaccggcccagcgaggtgtccaacagattcagcggcagcaagagcggcaacaccgccagc600
ctgacaatcagcggactgcaggccgaggacgaggccgactactactgcagcagctacacc660
accggcagcagagccgtgtttggcggaggcaccaagctgacagtgctgggcaccacgacg720
ccagcgccgcgaccaccaacaccggcgcccaccatcgcgtcgcagcccctgtccctgcgc780
ccagaggcgtgccggccagcggcggggggcgcagtgcacacgagggggctggacttcgcc840
tgtgatatctacatctgggcgcccttggccgggacttgtggggtccttctcctgtcactg900
gttatcaccctttactgcaaacggggcagaaagaaactcctgtatatattcaaacaacca960
tttatgagaccagtacaaactactcaagaggaagatggctgtagctgccgatttccagaa1020
gaagaagaaggaggatgtgaactgagagtgaagttcagcaggagcgcagacgcccccgcg1080
tacaagcagggccagaaccagctctataacgagctcaatctaggacgaagagaggagtac1140
gatgttttggacaagagacgtggccgggaccctgagatggggggaaagccgagaaggaag1200
aaccctcaggaaggcctgtacaatgaactgcagaaagataagatggcggaggcctacagt1260
gagattgggatgaaaggcgagcgccggaggggcaaggggcacgatggcctttaccagggt1320
ctcagtacagccaccaaggacacctacgacgcccttcacatgcaggccctgccccctcgc1380
<210>19
<211>1458
<212>dna
<213>人工序列(artificialsequence)
<400>19
gccctgcctgtgacagccctgctgctgcctctggctctgctgctgcatgccgctagaccc60
gctcgacattgttctctcccagtctccagcaatcatgtctgcatctccaggggagaaggt120
caccatatcctgcagtgccagctcaagtgtaagttatatgtactggtaccagcagaacaa180
ggatcctcccccaaaccctggatttatcgcacatccaacctggcttctggagtccctgct240
cgcttcagtggcagtgggtctgggacctcttactctctcacaatcagcagcatggaggct300
gaagatgctgccacttattactgccagcagtatcatagttacccacccacgttcggtgct360
gggaccaagctggagctgaaatcctctggtggcggtggctcgggcggtggtgggggtggt420
tcctctagatcttccctcgaggtgaagctggtggagtctggacctgagctgaagaagcct480
ggagagacagtcaagatctcctgcaaggcttctggttataccttcacagactattcaatg540
cactgggtgaatcaggctccaggaaagggtttaaagtggatgggctggataaacactgag600
actggtgagccatcatatgcagatgacttcaagggacggtttgccttctctttggaaacc660
tctgccagcactgcctatttgcagatcaacaacctcaaaaatgaggacacggctacatat720
ttctgtgctaccgattacggggactactttgactactggggccaaggcaccactctcaca780
gtctcctcaaccacgacgccagcgccgcgaccaccaacaccggcgcccaccatcgcgtcg840
cagcccctgtccctgcgcccagaggcgtgccggccagcggcggggggcgcagtgcacacg900
agggggctggacttcgcctgtgatatctacatctgggcgcccttggccgggacttgtggg960
gtccttctcctgtcactggttatcaccctttactgcaaacggggcagaaagaaactcctg1020
tatatattcaaacaaccatttatgagaccagtacaaactactcaagaggaagatggctgt1080
agctgccgatttccagaagaagaagaaggaggatgtgaactgagagtgaagttcagcagg1140
agcgcagacgcccccgcgtacaagcagggccagaaccagctctataacgagctcaatcta1200
ggacgaagagaggagtacgatgttttggacaagagacgtggccgggaccctgagatgggg1260
ggaaagccgagaaggaagaaccctcaggaaggcctgtacaatgaactgcagaaagataag1320
atggcggaggcctacagtgagattgggatgaaaggcgagcgccggaggggcaaggggcac1380
gatggcctttaccagggtctcagtacagccaccaaggacacctacgacgcccttcacatg1440
caggccctgccccctcgc1458
<210>20
<211>1440
<212>dna
<213>人工序列(artificialsequence)
<400>20
gccctgcctgtgacagccctgctgctgcctctggctctgctgctgcatgccgctagaccc60
cagagcgtgctgacacagcctgcctccgtgtctggctctcctggccagtccatcaccatc120
agctgtaccggcaccagctccgacgtgggcggctacaattacgtgtcctggtatcagcag180
catcccggcaaggcccccaagctgatgatctacgacgtgaacaaccggcccagcgaggtg240
tccaacagattcagcggcagcaagagcggcaacaccgccagcctgacaatcagcggactg300
caggccgaggacgaggccgactactactgcagcagctacaccaccggcagcagagccgtg360
tttggcggaggcaccaagctgacagtgctgggcggaggcggaggatctggcggcggagga420
agttctggcggagggtctcagagcgtgctgacacagcctgcctccgtgtctggctctcct480
ggccagtccatcaccatcagctgtaccggcaccagctccgacgtgggcggctacaattac540
gtgtcctggtatcagcagcatcccggcaaggcccccaagctgatgatctacgacgtgaac600
aaccggcccagcgaggtgtccaacagattcagcggcagcaagagcggcaacaccgccagc660
ctgacaatcagcggactgcaggccgaggacgaggccgactactactgcagcagctacacc720
accggcagcagagccgtgtttggcggaggcaccaagctgacagtgctgggcaccacgacg780
ccagcgccgcgaccaccaacaccggcgcccaccatcgcgtcgcagcccctgtccctgcgc840
ccagaggcgtgccggccagcggcggggggcgcagtgcacacgagggggctggacttcgcc900
tgtgatatctacatctgggcgcccttggccgggacttgtggggtccttctcctgtcactg960
gttatcaccctttactgcaaacggggcagaaagaaactcctgtatatattcaaacaacca1020
tttatgagaccagtacaaactactcaagaggaagatggctgtagctgccgatttccagaa1080
gaagaagaaggaggatgtgaactgagagtgaagttcagcaggagcgcagacgcccccgcg1140
tacaagcagggccagaaccagctctataacgagctcaatctaggacgaagagaggagtac1200
gatgttttggacaagagacgtggccgggaccctgagatggggggaaagccgagaaggaag1260
aaccctcaggaaggcctgtacaatgaactgcagaaagataagatggcggaggcctacagt1320
gagattgggatgaaaggcgagcgccggaggggcaaggggcacgatggcctttaccagggt1380
ctcagtacagccaccaaggacacctacgacgcccttcacatgcaggccctgccccctcgc1440
<210>21
<211>20
<212>prt
<213>人工序列(artificialsequence)
<400>21
alaleuprovalthralaleuleuleuproleualaleuleuleuhis
151015
alaalaargpro
20
<210>22
<211>60
<212>dna
<213>人工序列(artificialsequence)
<400>22
gccctgcctgtgacagccctgctgctgcctctggctctgctgctgcatgccgctagaccc60
- 还没有人留言评论。精彩留言会获得点赞!