一种基于CRISPR/Cas12a快速精准检测非洲猪瘟病毒的方法及应用与流程
本发明属于病原检测技术领域。更具体地,涉及一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的方法及应用。
背景技术:
非洲猪瘟(africanswinefever,asf)是由非洲猪瘟病毒(africanswinefevervirus,asfv)感染家猪和野猪引起的急性、热性、高度接触性传染病,急性型表现为高热、精神沉郁、厌食、皮肤发绀、脾脏肿大出血,发病率和死亡率高达100%。自2018年8月非洲猪瘟进入中国以来,该病迅速席卷全国,造成巨大的经济损失,全国能繁母猪急剧下降,促使我国养猪业及动保相关企业发生颠覆性改变。该病目前尚无疫苗,也无有效抑制非洲猪瘟病毒药物,故早期监测诊断和生物安全对非洲猪瘟防控非常重要。
相比较于传统病原鉴定方法,核酸检测技术是早期检测诊断的利器。现已开发出不少非洲猪瘟病毒核酸检测方法,如荧光定量pcr、普通pcr、lamp等,但是这些方法均需昂贵的设备,且需要标准化的实验室和专业技术人员进行操作,反应时间长,难以满足猪场一线要求,对于病毒含量极低的情况无法实现早期监测。如何更加快速、简便、准确、廉价的检测,是非洲猪瘟病毒核酸检测未来的发展方向。
2018年,doudna教授实验室向检测体系中加入crrna和cas12a蛋白,当靶标dna存在时,cas12a与crrna以及靶标dna形成三元复合体,该复合物行使其trans切割的活性并切割带荧光信号标记的单链dna(两头分别连有发光基团和淬灭基团,被切断后发光基团可以发光),从而发出荧光。因此,通过检测荧光即可得知待检测体系中是否含有靶标dna分子。
然而,对于非洲猪瘟的防控早期监控预防是极其重要的,一旦非洲猪瘟病毒形成一定规模以后,即使检测到也难有好的手段彻底防控。因此,针对非洲猪瘟病毒的防控,对于无法确定病毒核酸阴阳性的病毒含量极低样品的成功检测,是很关键的,这受的诸多因素的影响,目前上述doudna教授团队开发的方法尚未进行详细研究,即该技术是否能够运用于弱阳性及很难/无法确定阴阳性样品的检测并准确判定样品阴阳性未知,尚未有相关的深入研究。
技术实现要素:
本发明要解决的技术问题是克服现有非洲猪瘟病毒早期监测防控技术的缺陷和不足,提供一种高灵敏度、高特异性、操作方法简单、快速、精准检测非洲猪瘟病毒的方法。本发明建立的检测方法能够运用于猪场生产一线,无需昂贵仪器设备和专业标准实验室,对非洲猪瘟早期监测诊断与防控具有重要意义。
本发明的目的是提供一种检测效果最理想、灵敏度精准度最高的用于非洲猪瘟病毒检测的crrna。
本发明另一目的是提供一种检测非洲猪瘟病毒的crispr/cas12a系统。
本发明再一目的是提供一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的方法。
本发明再一目的是提供一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的试剂盒。
本发明再一目的是提供一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的试纸条。
本发明上述目的通过以下技术方案实现:
本发明研究发现,当asf病毒核酸与cas12a、crrna形成三元复合体时,该复合物中cas12a的ruvc结构域行使dnase活性,切割带荧光信号标记的单链dna(ssdnareporter),通过检测荧光即可得知待检样品中是否含有asf病毒核酸。基于此,本发明构建了一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的方法,设计了精准度最高、效率最高、灵敏度最高的优质crrna,保证了asf病毒检测效果。
因此,本发明提供一种用于非洲猪瘟病毒检测的crrna,具体是crrna1-crrna19中的任一种或任几种的组合,crrna1-crrna19的序列分别如seqidno.1-19所示。
所述crrna在检测非洲猪瘟病毒中的应用,以及在制备非洲猪瘟病毒检测产品中的应用,也均应在本发明的保护范围之内。
基于此还提供一种检测非洲猪瘟病毒的crispr/cas12a系统,包括上述crrna及其组合。
具体地,所述crispr/cas12a系统还包括rpa扩增引物对rpa-f/rpa-r,序列如seqidno.20-21所示。
优选地,所述crispr/cas12a系统还包括ssdnafq-labeledreporter,序列为:5′-fam-ttatt-bhq1-3′。
另外,所述crispr/cas12a系统还包括rpa扩增体系和crispr/cas12a检测体系所需试剂。
具体地,作为一种可选择的方案,所述rpa扩增体系如下:
所述crispr/cas12a检测体系如下:
另外,基于上述成果,包含所述crispr/cas12a系统的非洲猪瘟病毒检测试剂盒,利用该系统基于crispr/cas12a快速精准检测非洲猪瘟病毒的方法,以及基于crispr/cas12a检测原理、利用所述crispr/cas12a系统的试剂构建得到的非洲猪瘟病毒检测试纸条等产品,也均应在本发明的保护范围之内。
本发明具有以下有益效果:
本发明首次研究提供了一种基于crispr/cas12a能够快速、精准检测asfv的技术,这种技术可作为早期监测诊断asfv的检测方法。其最大优势为灵敏度高。目前asfv公认最好的检测方法为荧光定量pcr,通过试验比对,我们建立的检测方法比荧光定量pcr至少高10倍(目前荧光定量pcr最低检测浓度为10copy/μl病毒粒子,而基于crispr/cas12a技术最低检测浓度为1copy/μl病毒粒子)。
因此,本发明建立的检测方法再一优势为可针对对于病毒含量极低的弱阳性及疑似阳性样品实现高效检测,只需适当增加反应时间即可确定asfv核酸阳性还是阴性。目前荧光定量pcr的缺陷为:对于病毒含量极低即ct值在30-37的样品无法确定asfv核酸阴阳性,即使反应时间延长,结果仍为可疑,给asf早期监测及防控带来不确定性。本发明建立的检测方法,对于疑似病毒核酸阳性样品,只要增加反应时间,即可提高荧光数值,进而确定样品阴阳性,极大提高猪场一线asf早期监测。
本发明建立的检测方法另一优势为筛选到效果最好的crrna,使本发明建立的方法灵敏度进一步提高。crispr/cas12a检测方法的核心在于crrna,故crrna与灵敏度、精准度直接相关。在19个crrna中,通过crispr/cas12a检测,crrna5、crrna15荧光值最高,说明这2个效果最好,灵敏度最高。
本发明建立的检测方法再一优势为成本低,无需昂贵仪器设备。目前荧光定量pcr仪器昂贵,普通国产价格在15万左右,而本发明建议的检测方法只需水浴锅或恒温培养箱及荧光检测仪,所有仪器设备成本不到1万,而且适合猪场一线使用,不需专业规范的实验室。
本发明建立的检测方法再一优势为检测时间短。目前荧光定量pcr反应时间为1.5-2h,而本发明建立的方法:恒温扩增10min,再用cas12a检测荧光,20min,共计30min。故本发明建立的检测方法更有利于早期快速检测asfv,对早期asfv防控非常重要。
附图说明
图1为19个crrna对临床2份asf病毒核酸阳性样品crispr/cas12a检测15min荧光值测定结果。
图2为19个crrna对临床2份asf病毒核酸阳性样品crispr/cas12a检测30min荧光值测定结果。
图3为针对临床17份样品,crispr/cas12a检测方法荧光值测定结果。
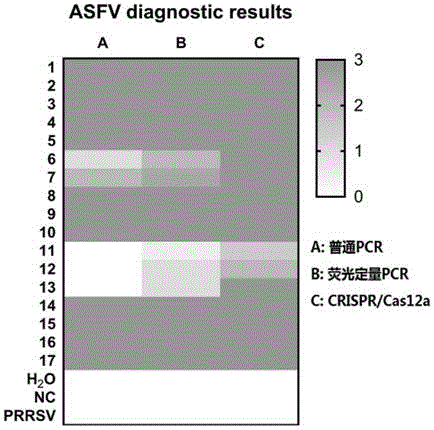
图4为通过热图(heatmap)展示临床17份样品普通pcr、荧光定量pcr、crispr/cas12a三种检测方法检测结果比较。
图5为crispr/cas12a检测asfv特异性分析。
图6为阳性血清10倍倍比稀释后,crispr/cas12a检测方法荧光值测定结果。
图7为阳性血清10倍倍比稀释后,荧光定量pcr扩增曲线。
图8为阳性血清10倍倍比稀释后,荧光定量pcrct值。
图9为阳性血清10倍倍比稀释后,crispr/cas12a不同反应时间荧光值测定结果。
具体实施方式
以下结合具体实施例来进一步说明本发明,但实施例并不对本发明做任何形式的限定。除非特别说明,本发明采用的试剂、方法和设备为本技术领域常规试剂、方法和设备。
除非特别说明,以下实施例所用试剂和材料均为市购。
本发明以下实施例的统计学分析:所有试验至少3次独立重复,结果采用平均值和标准误表示,使用单因素方差分析和t检测分析。所有统计分析均采用以p<0.05作为具有显著统计学差异的检验标准,分析软件为spss16.0和graphpadprism5。
实施例1crrna的设计
crispr/cas12a检测方法的核心在于crrna,故crrna质量与检测方法灵敏度、精准度直接相关。为了筛选效率最高的crrna,针对asfvvp72gene(genbankaccessionno.mh766894.1),我们设计了19个ssdna,并制备了19个crrna(序列如seqidno.1-19所示)。
(1)退火体系如表1
表1
将上述组分加入200μl离心管中,混匀并离心。放入pcr仪中进行退火反应:37℃,30min;95℃,5min;每分钟降5℃,至25℃,获得templatedna。ssdnasense、ssdnaantisense由上海生工合成。
(2)转录
用megashortscripttmt7transcriptionkit(invitrogen,usa)进行转录,反应体系如表2:
表2
将上述组分加入200μl离心管中,轻弹混匀并离心。置于37℃恒温水浴锅中,反应3个小时;然后每支管子加入1μlturbodnase,37℃下,共孵育15min,获得crrna。
(3)纯化crrna
用rnaclean&concentratortm-5(zymoresearch)试剂盒进行crrna的纯化,并在nanodrop上测定浓度,纯化获得的crrna冻存于-80℃冰箱。
实施例2crispr/cas12a检测asfv方法的建立
1、目的片段扩增
(1)提取病毒dna
取200μl血清样品,用rapureviralrna/dnakit(magen,china),按照操作步骤进行处理,提取病毒核酸。
(2)rpa扩增
设计用于rpa扩增的rpa-f/rpa-r,序列如seqidno.20-21所示。
rpa扩增体系如表3
表3
将上述46μl混合液加到装有冻干酶粉的twistampnfokit(twistdxtm,cambridge,unitedkingdom)反应管中,将冻干酶粉吹打至完全溶解,然后向反应管中加入4μl醋酸镁溶液,混匀,将反应管放入37℃恒温培养箱中培养10min,完成rpa扩增。rpa扩增产物进行1.5%的琼脂糖凝胶核酸电泳,观察条带位置和明亮深浅。rehydrationbuffer购自twistdxtm,cambridge,unitedkingdom.
3、crispr/cas12a检测asfv
crispr/cas12a检测体系如表4
表4
将上述组分依次加入384孔板中,封膜,避光离心后,放入37℃恒温生化培养箱中,反应1小时后,用biotek酶标仪读取荧光值。新合成的fluorophorequencher(fq)-labeledreporter序列为,5`6-fam-ttatt-3`bhq1,其检测条件为λex:485nm;λem:535nm。
实施例3筛选效率最高的crrna
对临床2份asf病毒核酸阳性样品用rapureviralrna/dnakit(magen,china),按照操作步骤进行处理,提取病毒核酸。再按实施例1中rpa扩增方法和条件,进行rpa扩增。最后按照实施例1中crispr/cas12a检测asfv方法和条件进行反应,反应体系中crrna分别用上述制备的19个crrna,反应时间为15或30min,反应结束后用biotek酶标仪读取荧光值。
结果如图1、图2所示:在反应时间15、30min后,crrna5、crrna15荧光值最高,说明在19个crrna中,这2个效果最好,灵敏度最高。
实施例4临床样本的crispr/cas12a检测
利用crrna5和实施例1的检测方法,对17份待检临床样品(asf病毒核酸阳性)进行处理、检测。
结果如图3、图4所示:通过crispr/cas12a检测发现,待检临床17份样品均为asf病毒核酸阳性,且部分样品普通pcr跑胶图肉眼无法辨别阴阳性,荧光定量pcr部分样品ct值偏高,通过热图可知crispr/cas12a检测方法灵敏度最高。
实施例5crispr/cas12a检测asfv特异性分析
实验材料:猪繁殖与呼吸综合征病毒(prrsv)、猪瘟病毒(csfv)、猪圆环病毒2型(pcv2)、猪伪狂犬病毒(prv),保存于本实验室。
用rapureviralrna/dnakit(magen,china),按照操作步骤进行处理,分别提取以上病毒与asfv核酸。再按实施例1中rpa扩增方法和条件,进行rpa扩增。最后按照实施例1中crispr/cas12a检测asfv方法和条件进行反应,反应体系中rpa模板分别用上面不同的病毒rpa扩增产物,反应结束后用biotek酶标仪读取荧光值。
结果如图5所示:prrsv、csfv、pcv2、prv荧光值极低,而asfv样品荧光值在8000以上,且与prrsv、csfv、pcv2、prv有极显著差异(p<0.0001)。以上结果表明,本发明构建的检测asfv方法具有很强的特异性,与其他病毒无交叉反应。
实施例6crispr/cas12a检测asfv灵敏度分析及与荧光定量pcr比较
1、将已知病毒拷贝数阳性血清进行10倍倍比稀释,直至10的10次方。稀释好的血清用rapureviralrna/dnakit(magen,china),按照操作步骤进行处理,提取病毒核酸。再按实施例1中rpa扩增方法和条件,进行rpa扩增。最后按照实施例1中crispr/cas12a检测asfv方法和条件进行反应,反应体系中rpa模板分别用上面不同稀释度的病毒rpa扩增产物,反应结束后用biotek酶标仪读取荧光值。
结果如图6所示:随着稀释度的升高,荧光值下降,当稀释到106,与阴性对照比,荧光值具有显著差异,提示样品稀释到106,本发明建立的检测方法仍然检测到病毒核酸。
2、荧光定量pcr是目前公认检测asfv灵敏度最高的方法。我们把上述倍比稀释血清,用荧光定量pcr方法检测。采用文献报道方法(preclinicaldiagnosisofafricanswinefeverincontact-exposedswinebyareal-timepcrassay),反应条件、反应体系、引物参照上述文献。
结果如图7、图8所示:随着稀释度的升高,ct值变大,当稀释到105,有扩增曲线,平均ct值为33.52,稀释到106时,无扩增曲线和ct值,即样品稀释到105为荧光定量pcr最低检测浓度。
综上所述,本发明建立的检测方法与荧光定量pcr相比,灵敏度高出一个数量级(即高10倍)。
实施例7针对弱阳性及疑似阳性样品crispr/cas12a反应时间延长即可确定asfv核酸阴阳性
目前荧光定量pcr的缺陷为:对于病毒含量极低即ct值在30-37的样品无法确定asfv核酸阴阳性,即使反应时间延长,结果仍为可疑,给asf早期监测及防控带来不确定性。本发明建立的检测方法,对于疑似病毒核酸阳性或病毒含量极低的样品,只要增加反应时间,即可提高荧光值,进而确定样品阴阳性,极大提高猪场一线asf早期监测。
将已知病毒拷贝数阳性血清进行10倍倍比稀释,直至10的3次方。稀释好的血清用rapureviralrna/dnakit(magen,china),按照操作步骤进行处理,提取病毒核酸。再按实施例1中rpa扩增方法和条件,进行rpa扩增。最后按照实施例1中crispr/cas12a检测asfv方法和条件进行反应,反应体系中rpa模板分别用上面不同稀释度的病毒rpa扩增产物,反应时间为10、20、30、40、50、60min,反应结束后用biotek酶标仪读取荧光值。
结果如图9所示:当样品不稀释即100,反应时间25min,荧光值基本达到峰值。但样品稀释到101、102、103时,随着反应时间的延长,不同稀释度样本荧光值升高,特别是稀释到102、103时,更明显,与反应时间呈正相关。
结果表明,利用本发明的检测方法,当待检样品病毒含量极低时,只要通过提高反应时间,即可确定asf病毒核酸阴阳性,对asfv早期监测与防控非常重要。同时prrsv阴性对照随着反应时间延长,荧光值基本不变,表明试验结果可信。
上述实施例为本发明较佳的实施方式,但本发明的实施方式并不受上述实施例的限制,其他的任何未背离本发明的精神实质与原理下所作的改变、修饰、替代、组合、简化,均应为等效的置换方式,都包含在本发明的保护范围之内。
sequencelisting
<110>中山大学
<120>一种基于crispr/cas12a快速精准检测非洲猪瘟病毒的方法及应用
<130>
<160>21
<170>patentinversion3.3
<210>1
<211>42
<212>dna
<213>crrna1
<400>1
cauuaaagaugauucacaucuauuaggauauuuguauauaag42
<210>2
<211>46
<212>dna
<213>crrna2
<400>2
cauuaaagaugauucacaucuaucucgucuguaaucaaaaaguagc46
<210>3
<211>44
<212>dna
<213>crrna3
<400>3
cauuaaagaugauucacaucuauccccaauguuuguccaauaac44
<210>4
<211>42
<212>dna
<213>crrna4
<400>4
cauuaaagaugauucacaucuacgcuacguucgaaauaccac42
<210>5
<211>46
<212>dna
<213>crrna5
<400>5
cauuaaagaugauucacaucuagcuacguucgaaauaccacuauuu46
<210>6
<211>42
<212>dna
<213>crrna6
<400>6
cauuaaagaugauucacaucuaaccacuauuucgcgagcggc42
<210>7
<211>45
<212>dna
<213>crrna7
<400>7
cauuaaagaugauucacaucuaccccaaacuccagguaaugucga45
<210>8
<211>39
<212>dna
<213>crrna8
<400>8
cauuaaagaugauucacaucuaggacgacaaaccuauaa39
<210>9
<211>44
<212>dna
<213>crrna9
<400>9
cauuaaagaugauucacaucuaguagccauucuuauccaaacga44
<210>10
<211>46
<212>dna
<213>crrna10
<400>10
cauuaaagaugauucacaucuaaagcuaaacugaguuucacccaag46
<210>11
<211>46
<212>dna
<213>crrna11
<400>11
cauuaaagaugauucacaucuaguaguuucaagacgucgagaaugu46
<210>12
<211>46
<212>dna
<213>crrna12
<400>12
cauuaaagaugauucacaucuauccuaucucuaugucgagaagguc46
<210>13
<211>46
<212>dna
<213>crrna13
<400>13
cauuaaagaugauucacaucuaguaguuauuggacaaacauugggg46
<210>14
<211>44
<212>dna
<213>crrna14
<400>14
cauuaaagaugauucacaucuauugguaccaaauaggguccuca44
<210>15
<211>46
<212>dna
<213>crrna15
<400>15
cauuaaagaugauucacaucuaagugguauuucgaacguagcguuu46
<210>16
<211>43
<212>dna
<213>crrna16
<400>16
cauuaaagaugauucacaucuaucaguuuagcuucuuugugua43
<210>17
<211>44
<212>dna
<213>crrna17
<400>17
cauuaaagaugauucacaucuaagaauaacgauugcuacccuuc44
<210>18
<211>39
<212>dna
<213>crrna18
<400>18
cauuaaagaugauucacaucuaguaguuucaagacgucg39
<210>19
<211>39
<212>dna
<213>crrna19
<400>19
cauuaaagaugauucacaucuaagcuauucuaacuaugg39
<210>20
<211>30
<212>dna
<213>上游引物rpa-f
<400>20
atatgaccactgggttggtattcctcccgt30
<210>21
<211>30
<212>dna
<213>下游引物rpa-r
<400>21
atcaacaccgagattggcacaagttcggac30
- 还没有人留言评论。精彩留言会获得点赞!