提高特异性的检测犬副流感的反应液、引物对、探针及试剂盒的制作方法
本发明涉及分子生物学技术领域,尤其涉及一种提高反转录核酸链式扩增反应特异性和敏感性的检测犬副流感的反应液、引物对、探针及试剂盒。
背景技术:
反转录pcr(rt-pcr)是聚合酶链式反应(pcr)的一种广泛应用的变形。在rt-pcr中,一条rna链被反转录成为互补dna,再以此为模板通过pcr进行dna扩增。rt-pcr的指数扩增是一种很灵敏的技术,可以检测很低拷贝数的rna。rt-pcr广泛应用于rna病毒检测、遗传病的诊断,并且可以用于定量监测某种rna的含量。
rt-pcr的关键步骤是在rna的反转录,常用的反转录酶有两种,即鸟类成髓细胞性白细胞病毒(以下amv)反转录酶和莫罗尼鼠类白血病病毒(以下mmlv)反转录酶,由于反转录酶无修正错配活性,反转录产生的cdna容易形成错配,导致后续的pcr反应特异性和敏感性降低。
reca蛋白首先与单链dna结合,在atp提供能量的条件下形成一条dna-蛋白质细丝,活化的reca蛋白将双螺旋解旋和分离,同时企图将它结合的单链与被解旋区域退火,如此继续下去,直到找到互补顺序,一旦有一小部份被真正“退火”,atp供应的能量就会继续驱使配对反应趋于完成,其方向是5’→3’,当新的杂交双链形成时,reca蛋白即从原来的单链掉下来。
我们在研究中发现在反转录反应中添加reca蛋白和atp,可提高反转录产物的特异性,反转录产物经过测序确定无碱基错配。
犬副流感病毒感染犬的主要的呼吸道传染病。临床表现发热、咳嗽、流涕等症状,病理变化以卡他性鼻炎和支气管炎为特征,研究表明犬副流感病毒可引起急性脑髓炎和脑内积水,临床表现后躯麻癖和运动失调等症状,随着宠物数量的增加,犬副流感病毒检测试剂的需求也越来越大,对犬流感病毒核酸检测试剂的特异性和敏感性也提出了更高的要求。
技术实现要素:
本发明的目的在于提供一种提高反转录核酸链式扩增反应特异性的检测犬副流感的反应液、引物对、探针及试剂盒,从而解决现有技术中反转录反应特异性差、rt-pcr非特异性扩增明显;犬副流感病毒检测试剂-包括核酸检测试剂特异性较差的问题。
为了实现上述目的,本发明采用的技术方案如下:
第一方面,本发明提供一种提高反转录反应特异性和敏感性的反转录反应液,反应液中含有reca蛋白以及为reca蛋白提供能量的atp。
第二方面,本发明提供一种提高反转录核酸链式扩增特异性和敏感性的rt-pcr反应液,反应液添加反转录酶、taq酶、dntp、特异性引物、缓冲液等常规成分以外,还添加了reca蛋白以及为reca蛋白提供能量的atp。
第三方面,本发明提供一种用于检测犬副流感基因的引物对,包括有:在犬流感病毒基因保守序列设计的碱基序列如seqidno:1、seqidno:2所示的引物;其中,所述碱基序列的5’端碱基具有氨基修饰基团,以提高引物tm值。
第四方面,本发明提供一种用于检测犬副流感病毒基因的探针,包括有针对犬副流感病毒保守序列设计的碱基序列如seqidno:3所示的荧光探针;其中,所述碱基序列中的一个碱基具有氨基修饰基团,提高了探针的tm值。
第五方面,本发明提供一种检测犬副流感病毒的试剂盒,包括引物对、荧光探针选择、配制rt-pcr反应体系、设置反应条件的步骤,其中,所述引物对采用上述的引物对,所述荧光探针采用上述的荧光探针。
在其中的实施例中,所述设置反应条件的步骤中,反转录反应温度设为42-50℃,反应温度设为60-63.2℃。
与现有技术相比,本发明具有以下有益效果:
本发明反转录反应液创造性的添加reca蛋白以及为其提供能量的atp,提高了反转录产物的特异性,提高了反转录反应效率,为提高rt-pcr反应的特异性提供了前提基础。
同时使用本发明rt-pcr体系提供犬副流感病毒检测用实时荧光rt-pcr试剂盒。
本发明试剂盒所用的引物和探针采用氨基修饰技术,提高引物探针的tm值,实现了缩短引物和探针长度,继而实现降低保守区域过短引起的引物探针设计难度,同时实现了在低gc区域设计的引物探针tm值过低,需要降低退火温度导致的pcr反应时间变长的问题,同时降低了引物探针设计难度。
本发明的引物,采用氨基基团修饰长度为20bp以下的特别是15-20bp引物的5’端,以提高引物tm值达到60℃左右,所扩增片段长度短于60bp的情况下能够实现特异性检测、高精度检测,且缩短检测时间。
本发明的荧光探针,使用氨基基团修饰长度为20bp以下的特别是15-20bp探针的一个碱基,以提高探针tm值达到68-70℃,这种设计保证了探针在60℃退火延伸时探针的杂交效率很低,最终达到特异性检测犬副流感病毒的目的。
本发明的检测方法,基于reca蛋白的特性和对引物对、探针的上述限定,与现有方法相比,对反转录反应产物的错配几乎减少到了最低,同时,与现有检测方法相比,变性时间仅需2-10s,退火延伸时间仅需2-30s,整个检测流程缩短了20-35min;进一步地,反应时间的缩短还进一步缩短了非100%相同序列探针杂交时间,最终达到特异性检测的目的。
附图说明
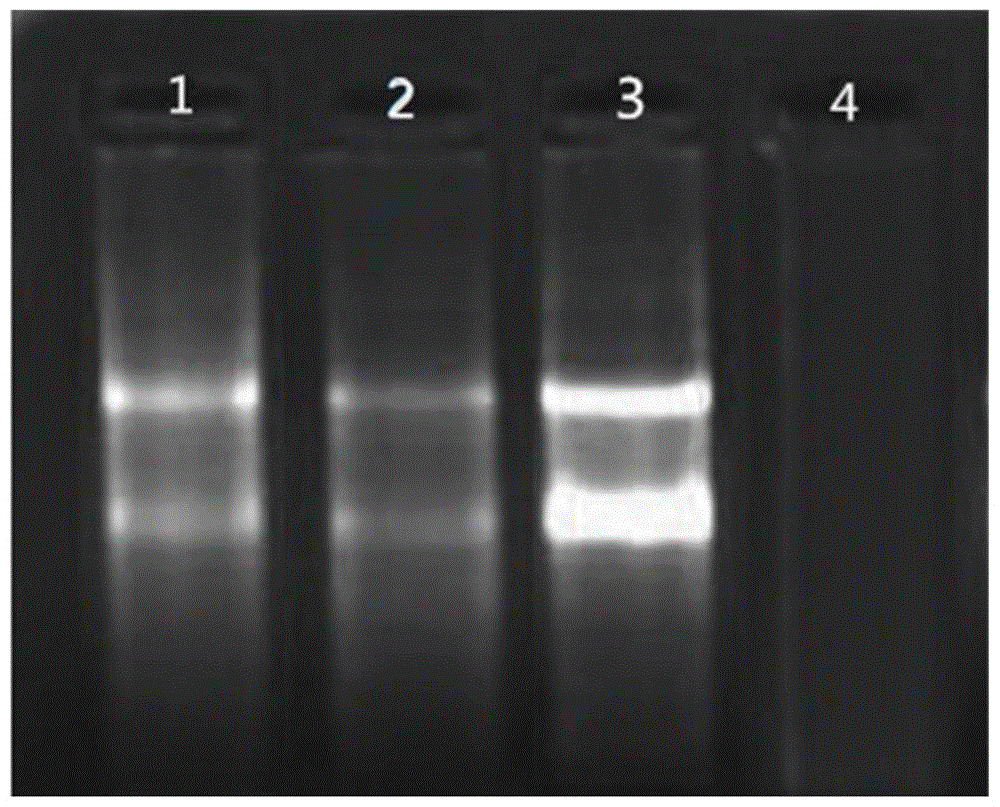
图1为本发明实施例1的电泳结果图:
图2为本发明实施例2的电泳结果图。
具体实施方式
为了能够更清楚地理解本发明的技术内容,特举以下实施例详细说明。应理解,这些实施例仅用于说明本发明而不用于限制本发明的范围。下列实施例中未注明具体条件的实验方法,通常按照常规条件,例如sambrook等人,分子克隆:实验室手册(newyork:coldspringharborlaboratorypress,1989)中所述的条件,或按照制造厂商所建议的条件。实施例中所用到的各种常用化学试剂,均为市售产品。
除非另有定义,本发明所使用的所有的技术和科学术语与属于本发明的技术领域的技术人员通常理解的含义相同。本发明的说明书中所使用的术语只是为了描述具体的实施例的目的,不用于限制本发明。本发明所使用的术语“和/或”包括一个或多个相关的所列项目的任意的和所有的组合。
实施例1
用于反转录反应的反应液的制备和反转录反应:
本实施例配置了常规反应液和本发明反应液,以ms2噬菌体保守区域(seqidno:4)作为模板进行反转录反应,反转录反应作用的引物对设计一组为100%相同序列引物(seqidno:5/seqidno:6),另一组错配一个碱基的引物(seqidno:7/seqidno:8)。
反转录反应使用宝生物公司smartmmlv反转录酶体系,一组按照试剂盒说明书进行配制反应液,一组按照试剂盒说明进行配制并添加了reca蛋白(浓度为0.01%)和atp(浓度为100ng/l),引物委托广州艾基生物合成。
引物对序列如下:
第一组:
正向引物(seqidno:5):tctttagcgagacgctac
反向引物(seqidno:6):tgcatggctgagattt
第二组
正向引物(seqidno:7):tctttagcgacacgctac
反向引物(seqidno:8):tgcatggctgcgattt
引物中大写字母为故意设计的错配位点。
反转录反应温度根据试剂盒说明书设定温度42℃进行60分钟。
表1
电泳结果图1所示:
进行三次验证,添加reca蛋白和atp后错配引物均不出现电泳条带,证实了reca和atp可以提高特异性。
使用cdna提取试剂精制添加reca蛋白组cdna后同模板ms2噬菌体送至广州艾基生物进行测序对比,证实与模板序列100%相同。
经过doe验证,确定reca添加量为0.001%~0.1%,最佳浓度为0.01%;确定atp添加量为10ng~1000ng,最佳浓度为100ng。
实施例2
用于pcr反应的反应液制备和pcr扩增:
本实施例使用实施例1中的cdna作为模板进行pcr,试剂使用宝生物公司takaraex
正向引物(seqidno:9):tgaaggcgtacactgcc
反向引物(seqidno:10):aagcatctcatatgcaccct
表2
电泳结果如图2所示。
进行三次验证,添加reca蛋白和atp后组均未见非特异性扩增,证实了使用reca蛋白和atp可提高rt-pcr特异性。
实施例3
用于检测犬副流感病毒的引物对、探针及其制备方法
本实施例针对犬副流感病毒保守区域设计了引物对。
从ncbi下载不同国家地区犬副流感基因组数据后使用dnaman进行对比分析,针对犬副流感基因保守区域设计引物对以及探针,引物对和探针序列如下:
正向引物(seqidno:1):5’g(氨基基团)tcctaatgcaggcatg3’;
反向引物(seqidno:2):5’c(氨基基团)aggttggtctggcg3’
荧光探针(seqidno:3):5’fam-atagt(氨基基团)gacttgcaagtgcatgact-bhq13’。
本实施例中,引物的制备包括:针对犬副流感病毒保守区域设计引物如seqidno:1、seqidno:2所示的引物,并用氨基基团对所述碱基序列的5’端碱基进行修饰,即得。
本实施例中,荧光探针的制备包括:针对犬副流感病毒保守区域设计探针如seqidno:3所示的探针,并用氨基基团对所述碱基序列的5’端开始第五个碱基(t)使用氨基基团修饰,即得。
制备上述引物对和探针的过程中,采用abi公司引物设计软件primerexpress分别对氨基基团修饰前的碱基序列、氨基基团修饰后的碱基序列的tm值进行测试,结果如下:
修饰前:正向引物碱基序列的tm值为48.8℃;反向引物碱基序列的tm值为50.3℃;荧光探针碱基序列的tm值为56.8℃。
修饰后:正向引物碱基序列的tm值为60.3℃;反向引物碱基序列的tm值为61.4℃;荧光探针碱基序列tm值为70.1℃。
修饰前碱基序列的tm值均比常规荧光pcr引物探针低,经过氨基基团修饰后的tm值显著提升。
本发明用于检测犬副流感病毒的引物对和荧光探针委托广州艾基生物科技有限公司合成。
实施例4
用于检测犬副流感病毒的试剂盒及验证:
本实施例针对犬副流感病毒设计了含有实施例1含reca蛋白和atp和实施例3引物对和探针的试剂盒以及验证,实验组含0.01%reca蛋白和100ng/l浓度的atp,对照组1不含reca蛋白和atp,对照组2为某公司犬副流感核酸检测试剂。
实验组反应体系如下:
最终反应体系25ul;
对照组1反应体系如下:
最终反应体系25ul;
对照组2按照试剂说明书进行配液及添加模板,最终反应体系20ul;
模板使用临床分离培养鉴定的犬副流感病毒。
2、反应程序按照对照组2试剂反应程序设定如下
42度45分
95度3分钟-1个循环
95度2秒,60度30秒-45循环
3、反应结果
反应结果请参见表3:1-cpiv为实验组,2-cpiv为对照组1,3-cpiv为对照组2,从表3结果可看出实验组空白对照未见阳性,特异性良好;对照组1空白对照ct值约为30,特异性差,实验组cт值比对照组2提前3个循环,敏感性明显提高。
表3
本发明上述实施例,采用添加reca蛋白和atp进行反转录反应,提高反转录反应的特异性,进而提高rt-pcr反应的特异性,在实验中发现在实时荧光rt-pcr反应液中添加reca蛋白和atp可提高敏感性,机制不明,推测为特异性提高后与模板rna序列完全相同的反转录产物比例增高,而提高了敏感性。氨基基团修饰的引物、探针,且长度均在20bp以下,扩增产物总长度小于60bp(实施例4总扩增长度为57bp),由此减少扩增所需时间,可实现快速pcr目的,最终达到同时保证特异性和敏感性。
以上所述实施例仅表达了本发明的几种实施方式,其描述较为具体和详细,但并不能因此而理解为对发明专利范围的限制。应当指出的是,对于本领域的普通技术人员来说,在不脱离本发明构思的前提下,还可以做出若干变形和改进,这些都属于本发明的保护范围。因此,本发明专利的保护范围应以所附权利要求为准。
序列表
<110>东莞博盛生物科技有限公司广州源博医药科技有限公司
<120>提高特异性的检测犬副流感的反应液、引物对、探针及试剂盒
<141>2019-05-21
<160>10
<170>siposequencelisting1.0
<210>1
<211>17
<212>dna
<213>artificialsequence
<400>1
gtcctaatgcaggcatg17
<210>2
<211>15
<212>dna
<213>artificialsequence
<400>2
caggttggtctggcg15
<210>3
<211>24
<212>dna
<213>artificialsequence
<400>3
atagtgacttgcaagtgcatgact24
<210>4
<211>1140
<212>rna
<213>genetictemplate
<400>4
ucuuuagcgagacgcuaccauggcuaucgcuguagguagccggaauuccauuccuaggag60
guuugaccugugcgagcuuuuaguacccuugauagggagaacgagaccuucguccccucc120
guucgcguuuacgcggacggugagacugaagauaacucauucucuuuaaaauaucguucg180
aacuggacucccggucguuuuaacucgacuggggccaaaacgaaacaguggcacuacccc240
ucuccguauucacggggggcguuaagugucacaucgauagaucaaggugccuacaagcga300
agugggucaucguggggucgcccguacgaggagaaagccgguuucggcuucucccucgac360
gcacgcuccugcuacagccucuucccuguaagccaaaacuugacuuacaucgaagugccg420
cagaacguugcgaaccgggcgucgaccgaaguccugcaaaaggucacccaggguaauuuu480
aaccuugguguugcuuuagcagaggccaggucgacagccucacaacucgcgacgcaaacc540
auugcgcucgugaaggcguacacugccgcucgucgcgguaauuggcgccaggcgcuccgc600
uaccuugcccuaaacgaagaucgaaaguuucgaucaaaacacguggccggcaggugguug660
gaguugcaguucgguugguuaccacuaaugagugauauccagggugcauaugagaugcuu720
acgaagguucaccuucaagaguuucuuccuaugagagccguacgucaggucgguacuaac780
aucaaguuagauggccgucugucguauccagcugcaaacuuccagacaacgugcaacaua840
ucgcgacguaucgugauaugguuuuacauaaacgaugcacguuuggcaugguugucgucu900
cuagguaucuugaacccacuagguauagugugggaaaaggugccuuucucauucguuguc960
gacuggcuccuaccuguagguaacaugcucgagggccuuacggcccccgugggaugcucc1020
uacaugucaggaacaguuacugacguaauaacgggugaguccaucauaagcguugacgcu1080
cccuacggguggacuguggagagacagggcacugcuaaggcccaaaucucagccaugcau1140
<210>5
<211>18
<212>dna
<213>artificialsequence
<400>5
tctttagcgagacgctac18
<210>6
<211>16
<212>dna
<213>artificialsequence
<400>6
tgcatggctgagattt16
<210>7
<211>18
<212>dna
<213>artificialsequence
<400>7
tctttagcgacacgctac18
<210>8
<211>16
<212>dna
<213>artificialsequence
<400>8
tgcatggctgcgattt16
<210>9
<211>17
<212>dna
<213>artificialsequence
<400>9
tgaaggcgtacactgcc17
<210>10
<211>20
<212>dna
<213>artificialsequence
<400>10
aagcatctcatatgcaccct20
- 还没有人留言评论。精彩留言会获得点赞!