一种颠茄AbPDS基因及其应用的制作方法
本发明属于vigs技术体系领域,具体是一种颠茄abpds基因及其在构建vigs体系中的应用。
背景技术
病毒诱导的基因沉默(virusinducedgenesilencing,vigs)能够诱导靶基因瞬时沉默从而应用于植物基因功能的研究,然而目前在颠茄上的vigs的体系尚未建立。病毒诱导的基因沉默目前已经广泛应用于植物基因功能的研究。该技术主要是以植物病毒为载体,导入靶基因的部分序列后,采用注射含病毒载体的菌体入植物细胞后,导入序列会与靶基因mrna形成双链最终导致靶基因降解,从而起到了基因沉默的作用。
技术实现要素:
鉴于此,本发明解决的技术问题是,本发明提供了一种在颠茄中实现瞬时基因沉默的vigs体系,为研究颠茄基因功能提供了重要的技术支持。
本发明在传统中药材颠茄中建立了病毒诱导的vigs体系。从颠茄中克隆了编码八氢番茄红素脱氢酶(phytoenedesaturase,pds)基因,通过vigs技术在颠茄中实现了pds基因表达沉默,从而抑制了颠茄叶绿素的生物合成,最终导致了叶片出现漂白现象。本发明首次克隆abpds基因并建立了颠茄的vigs体系,为研究颠茄基因的生物学功能提供了可靠的技术保障。
本发明采用的技术方案是:一种颠茄abpds基因,其dna序列为seqidno.1。
上述颠茄abpds基因,由dna序列为seqidno.2和dna序列为seqidno.3的上游引物和下游引物,进行pcr扩增获得。
pcr扩增的体系如下:
pcr程序为:95℃,3min→(95℃,变性30s→58℃,退火30s→72℃,延伸1min)×35循环→72℃,5min。
本发明所述abpds基因抑制叶绿素合成,用于构建vigs体系。所述vigs体系的构建步骤如下:
选择abpds基因中的770-bp片段克隆至ptrv2中,构建ptrv2-abpds重组质粒;ptrv2-abpds重组质粒是将所述abpds基因中的770-bp片段和trv2质粒分别用saci和kpni进行双酶切;再通过t4连接酶进行连接获得的。
分别将trv1以及trv2-abpds重组质粒转化进入农杆菌gv3101;
用trv1+trv2-abpds转化的农杆菌gv3101注射两周大颠茄幼苗,暗培养48h后移入光照培养,10d左右发现光漂白现象;
用分光光度法测定vigs介导的abpds沉默颠茄叶片的叶绿素含量,并用qpcr分析abpds基因的表达水平验证vigs效果。
本发明获得了颠茄abpds基因,验证了abpds基因的沉默具有抑制叶绿素合成的作用,为颠茄vigs体系的建立提供了重要的对照基因;颠茄vigs体系的构建有助于研究颠茄基因的生物学功能。
附图说明
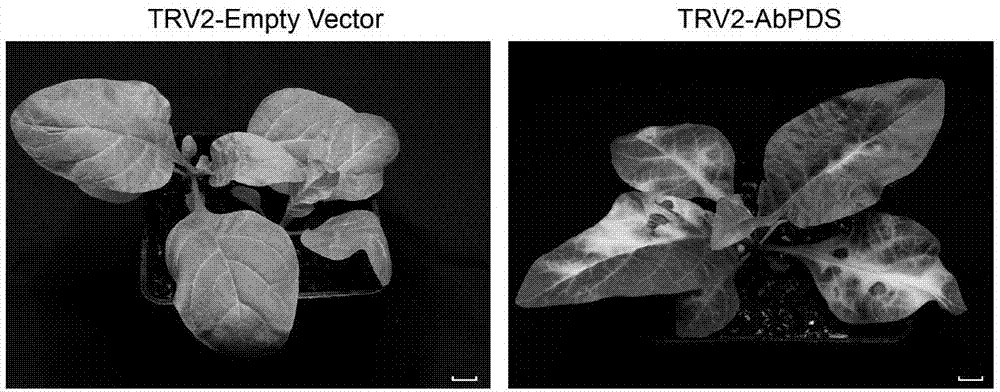
图1为vigs沉默abpds导致的漂白结果图;
图2为颠茄叶绿素含量图;
图3为abpds基因表达水平示意图。
具体实施方式
1.利用pcr技术克隆获得abpds基因全长(编码区),dna序列为seqno.1;如下所示:
其中下划线部分为本发明所选择的插入片段,用于构建ptrv2-abpds载体。
pcr反应中所用的引物:
序列为seqidno.2的上游引物(f-abpdscds):
5-atgtgtcataagttaaagattc-3
序列为seqidno.3的下游引物(r-abpdscds):
5-ctaaattacacttgcttctgcc-3
pcr步骤包括:
pcr体系如下:
pcr程序:95℃,3min→(95℃,变性30s→58℃,退火30s→72℃,延伸1min)×35循环→72℃,5min。
2.选择abpds基因中的770-bp片段克隆至vigs载体ptrv2中,构建ptrv2-abpds沉默载体并转入农杆菌gv3101;
插入片段,以高保真酶扩增获得的abpds编码序列为模板,采用下列引物进行pcr扩增:
f-abpds-trv2-saci:
5-gcgagctctcaatgcagtgcatcttgatcgc-3
r-abpds-trv2-kpni:
5-gcggtaccaagacagcaccttccattgaggc-3
将获得的770-bp片段和trv2质粒分别用saci和kpni进行双酶切;再通过t4连接酶进行连接获得ptrv2-abpds重组质粒
trv1质粒编码了病毒的复制蛋白、运动蛋白和转运因子,是vigs体系中不可或缺的质粒,在这个质粒的作用下,烟草脆裂病毒能够侵染植株。
分别将trv1,trv2以及trv2-abpds重组质粒转化进入农杆菌gv3101。
3.用trv1+trv2-abpds转化的农杆菌gv3101注射两周大颠茄幼苗,暗培养48h后移入光照培养,10d左右发现光漂白现象;
在实验中分别设置有对照组(trv1+trv2)以及实验组(trv1+trv2-abpds)。对照组结果如图1左图所示,实验组结果如图1右图所示。
4.用分光光度法测定vigs介导的abpds沉默颠茄叶片的叶绿素含量,并用qpcr分析abpds基因的表达水平验证vigs效果。
分光光度法测定叶绿素的方法如下:
色素的提取:剪去新鲜的白化叶片与对照组叶片,除去粗大的叶脉并剪成均一碎块,分别称重0.5g作为实验材料。在研钵中加入丙酮5毫升、少许石英砂、少许碳酸钙,然后研磨成匀浆待用。把匀浆放入离心管中离心,并用80%的丙酮冲洗研钵2次一并倒进离心管离心,4000rpm/6min。待离心后取上清液用80%的丙酮定容到20ml。
od值的测定:叶绿素a、叶绿素b分别在波长663nm、645nm处有最大吸收值,可采用光度法进行测定叶绿素的含量。取上述叶绿素提取液1毫升,稀释到5毫升,加入到比色皿中测定od663、od645的吸光值。将测定获得的吸光值分别用下列公式进行计算:
ρa=0.0127a663-0.00269a645
ρb=0.0229a663-0.00468a645
ρt=ρa+ρb
ρa:叶绿素a含量;ρb:叶绿素b含量;ρt:总叶绿素含量。
分别计算出叶绿素a、叶绿素b的含量和总的含量,在计算出每g所含的叶绿素含量。将白化的叶片叶绿素含量与对照组叶片叶绿素的含量进行比对。结果如图2所示,图中(a)表示叶绿素a的含量,(b)表示叶绿素b的含量,(c)表示的是总叶绿素含量。从图中可知在vigs植株中叶绿素a、叶绿素b和总叶绿素的含量较对照都有显著性地降低。
qpcr方法得到的结果如图3所示。
qpcr引物如下:
采用iqtm5多通道实时监测系统(bio-rad,usa)对上述处理样本进行了荧光定量pcr分析。按照
在200μlep管中加入以下反应试剂,正向引物和反向引物序列见上表所示:
反应程序为:95℃,30s;(95℃,5s;各基因最佳退火温度,30s;72℃,20s,检测荧光信号)×40个循环;各个组织的样本分别设3个机械重复1个阴性对照。为了判断荧光定量pcr的扩增是否特异,在上述扩增程序完成后进行融解曲线分析,程序如下:60℃到95℃逐渐升温,每间隔0.5℃读数一次,每次5s,连续记录荧光信号的变化。
sequencelisting
<110>重庆科技学院
<120>一种颠茄abpds基因及其应用
<160>9
<170>patentinversion3.3
<210>1
<211>1602
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(1602)
<223>abpds
<400>1
atgtgtcataagttaaagattcgtactccctatgccacgaccagaagattggcaaaggaa60
ttccatcctttaaaggtagtttgcgttgattatccaagaccagagctagacaatacagtt120
aactatttggaggctgcattcttatcatcatcattcggtactcctccatgcccaactaaa180
cctttggagattgttattgctggtgcaggtttgggtggtttgtctacagcaaaatatttg240
gcagatgctggtcacaaaccaatactgctagaggcaagggatgttttaggtggaaaggta300
gctgcatggaaagatgacgatggagattggtacgagactggtttgcacatattctttggg360
gcttacccaaatatgcagaacctgtttggagaactagggattaacgatcgattgcagtgg420
aaggaacattcaatgatatttgcaatgccaaacaagccaggagaattcagccgctttgat480
ttccccgaagctttacctgctcctttaaacggaattttggctatcctaaagaacaatgaa540
atgcttacatggccagagaaagtcaaatttgcaattggactcttgccagcaatgctgggt600
gggcaatcatatgttgaagctcaagacgggataagtgttaaggactggatgagaaaacaa660
ggtgttccggatagggtgacagatgaggtgttcatcgccatgtcaaaggcacttaacttc720
ataaaccctgaggagctctcaatgcagtgcatcttgatcgctttgaacagatttcttcag780
gagaaacatggttcaaaaatggcctttttagatggtagtcctcctgagcgactttgcatg840
ccgattgttgaacatatcgagtcaaaaggtggccaagtcagactgaactcacgaataaaa900
aagattgagctgaatgaggatggaagtgtcaagtgttttatactgaataatggtagtaca960
attgagggagatgctttcgtgtttgccactccagtggatattttcaagcttcttttgcct1020
gaagagtggaaagagatcccatatttccaaaagttggagaagttagtcggagtacctgtg1080
ataaatgtccatatatggtttgacagcaaactgaagaacacagaagataatctgctcttc1140
agcagaagcccactgctcagtgtgtatgctgacatgtccgtcacatgtaaggaatattac1200
aaccccaatcagtctatgttggaattggtttttgcacctgcagaagagtggatatctcgt1260
agtgactcggaaattattgatgctacaatgaaggaactagcaaagcttttccctgatgaa1320
atttcggcagatcagagcaaagcaaaaatattgaagtatcatgttgtcaaaactccaagg1380
tctgtttataaaactgtgccaggttgtgaaccctgtcggccgttgcaaagatccccaata1440
gaggggttctatttagctggtgactacacgaaacagaaatacttggcctcaatggaaggt1500
gctgtcttagcaggaaagctttgtgcgcaagctattgtgcaggattacgagttacttgtt1560
ggccggggccagaggaagttggcagaagcaagtgtaatttag1602
<210>2
<211>22
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(22)
<223>f-abpdscds
<400>2
atgtgtcataagttaaagattc22
<210>3
<211>22
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(22)
<223>r-abpdscds
<400>3
ctaaattacacttgcttctgcc22
<210>4
<211>31
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(31)
<223>f-abpds-trv2-saci
<400>4
gcgagctctcaatgcagtgcatcttgatcgc31
<210>5
<211>31
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(31)
<223>r-abpds-trv2-kpni
<400>5
gcggtaccaagacagcaccttccattgaggc31
<210>6
<211>20
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(20)
<223>f-qabpds
<400>6
aactgtgccaggttgtgaac20
<210>7
<211>20
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(20)
<223>r-qabpds
<400>7
gcttctgccaacttcctctg20
<210>8
<211>21
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(21)
<223>f-qabpgk
<400>8
tcgctcttggagaaggttgac21
<210>9
<211>23
<212>dna
<213>artificial
<220>
<221>misc_feature
<222>(1)..(23)
<223>r-qabpgk
<400>9
cttgtccgcaatcactacatcag23
- 还没有人留言评论。精彩留言会获得点赞!