猪小肠上皮细胞表达的PGC启动子及其应用的制作方法
本发明涉及动物基因工程领域,特别是涉及一种猪小肠上皮细胞表达的pgc启动子及其应用。
背景技术:
启动子是基因中重要的顺式作用元件,也是基因工程表达载体的一个重要组成部分,一般位于转录起始位点上游几十个碱基处。随着基因工程的发展,常常需要构建一种能高水平表达异源蛋白质的表达载体,而启动子对外源基因的表达水平影响很大,是基因工程中重要元件。因此,选择合适的启动子对于研究具有至关重要的作用。
小肠既是消化吸收的主要场所,也是重要的免疫屏障,高发肠炎及肠癌等疾病。例如,溃疡性结肠炎在我国的发病率约为万分之一,病毒性肠炎在美国每年有5100万人感染,但具体的发病原因和有效的治疗方法都有待进一步探究。因此,探明各类肠炎的发病机理,并找到合适的模式动物意义十分重大。
使外源性基因在组织中的高效、稳定表达是转基因动物研究和基因治疗的重要前提。在小肠表达病原体受体或抗病因子等外源基因是探究小肠相关疾病的重要手段。目前,关于猪小肠的基因表达调控序列还未有鉴定和应用,也没有关于猪小肠基因表达调控元件的猪肠道外源基因启动子的相关报道。
pgc基因位于猪基因组chromosome7,共有9个外显子和8个内含子,全长10.7kb。它编码的胃蛋白酶原c主要分布于胃及近端十二指肠,属于天冬氨酸蛋白酶家族,是消化功能逐渐成熟的一种标志。关于pgc基因的研究主要集中在胃部疾病方面,pgc表达变化可能与胃溃疡、胃炎和胃癌的发生有关。关于其启动子还未有相关报道。
技术实现要素:
本发明的目的在于提供一种能调控外源基因在猪小肠上皮细胞表达的pgc启动子。
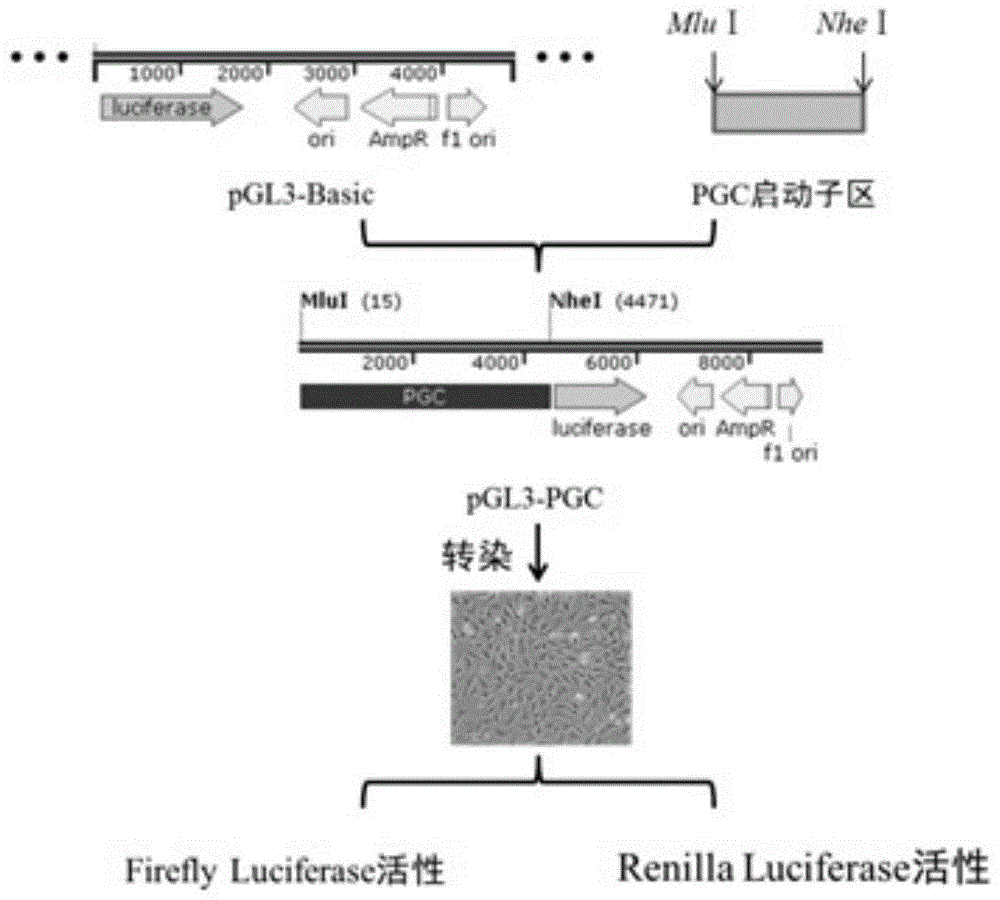
为达到以上目的,本发明通过以下方法获得了能在猪小肠上皮细胞表达的pgc启动子:(1)在线网站预测pgc可靠启动子区;(2)通过化学合成方法合成引物;(3)通过限制性酶切位点:mluⅰ和nheⅰ,将pgc启动子序列插入pgl3-basic载体,得到pgc-双荧光素酶重组质粒;(4)转染入e.coli大肠杆菌进行质粒扩增,提取质粒,测序验证;(5)转染入猪小肠上皮细胞(ipec-j2),进行双荧光素酶活性分析,利用双荧光素酶检测试剂盒检测荧光素酶活性,计算平均值和标准差。
具体而言,本发明提供了猪小肠上皮细胞表达的pgc启动子,其序列为:
1)seqidno.1所示的核苷酸序列;或
2)seqidno.1所示核苷酸序列经取代、缺失和/或添加一个或几个核苷酸所获得的具有同等功能的由1)衍生的核苷酸序列。
应当理解,本领域技术人员可根据本发明公开的启动子序列,在不影响其活性的前提下,取代、缺失和/或增加一个或几个核苷酸,得到所述启动子的突变序列。例如在非活性区段,在不改变启动子功能的情况下,进行碱基的取代、缺失和/或增加一个或几个核苷酸。
本发明提供了含有所述pgc启动子的生物材料,所述生物材料为载体、宿主细胞、宿主菌、转化植物细胞或表达盒。
本发明可选用本领域已知的各种载体,只要适合上述pgc启动子的表达即可,例如可以为市售的载体及质粒。
本发明提供了所述的pgc启动子或所述的生物材料在调控下游基因在猪小肠上皮细胞表达中的应用。
本发明提供了所述的pgc启动子或所述的生物材料在制备转基因动物中的应用,所述转基因动物为外源基因在猪小肠上皮细胞表达。
本发明提供了所述的pgc启动子或所述的生物材料在构建小肠疾病模型中的应用。
本发明提供了所述的pgc启动子或所述的生物材料在构建小肠疾病基因治疗系统中的应用。
本发明提供了用于克隆所述的pgc启动子的特异性引物对,包括:pgc-f:5'-cgacgcgttgatgtctgccacaggtgag-3',(seqidno.2)
pgc-r:5'-ctagctagctgccgcttatcgctctaatct-3'(seqidno.3)。
含有所述特异性引物对的试剂盒属于本发明的保护范围。
现有技术一直未有猪肠道外源基因启动子的相关报道,本发明首次分离了猪源pgc启动子,找到可以在猪肠道启动外源基因的启动子,其具有如seqidno.1所示的核苷酸序列。本发明利用该启动子表达双荧光素酶基因luc基因,结果发现猪源pgc启动子可在猪小肠上皮细胞中启动luc基因表达,说明所述启动子能够调控下游基因在猪小肠上皮细胞中表达,有利于构建稳定高效的小肠转录调控元件,在制备转基因动物和小肠疾病基因治疗研究中具有重要应用价值。
附图说明
图1为pgl3-pgc重组质粒的构建和荧光素酶检测过程示意图。
图2为pgl3-pgc重组质粒转化培养后进行菌液pcr的凝胶电泳图。
图3为双荧光素酶检测结果数据图表。
具体实施方式
以下实施例用于说明本发明,但不用来限制本发明的范围。
实施例1pgc启动子的获得与应用
利用基因工程技术,在ensembl数据库查找pgc基因序列,经promoter2.0predictionserver预测,得到可靠pgc启动子区。利用primerpremier5.0设计pgc启动子引物,以中国实验用小型猪基因组为模板进行pcr,扩增得到的片段与pgl3-basic载体连接。通过测序验证,实现pgc启动子-luc表达载体的重组。随后将重组质粒转染至ipec-j2细胞,检测荧光素酶活性。研究发现pgc启动子可达到启动luc(荧光素酶)的效果,示意图见图1。方法如下:
1.pgc可靠启动子区的预测
通过ensembl数据库查找pgc基因序列,下载其转录起始位点上下游各9000bp序列。查找第一外显子区,将﹣9000bp至+200bp范围序列提交到promoter2.0predictionserver在线网站进行预测,得到pgc可靠启动子区。
2.目的片段的获取
利用primerpremier5.0引物设计软件设计包含pgc可靠启动子区的引物。以中国实验用小型猪基因组为模板,上游引物为
5'-cgacgcgttgatgtctgccacaggtgag-3'(含mluⅰ酶切位点),下游引物为
5'-ctagctagctgccgcttatcgctctaatct-3'(含nheⅰ酶切位点),进行pcr,成功扩增出pgc启动子目的片段,长度为3553bp,为转录激活区域-3385至+168。利用omega试剂盒回收pgc启动子的dna片段。
3.pgl3-pgc重组质粒的构建
将pgc启动子片段与pgl3-basic质粒进行mluⅰ和nheⅰ双酶切,酶切体系为buffer2.15μl,质粒或片段2μg(根据浓度计算体积),nheⅰ2μl,用水补足50μl,混匀后37℃酶切3h,取3μl鉴定酶切效果。剩余47μl中加buffer3.110μl,mluⅰ5μl,用水补足100μl,混匀后37℃酶切4h,电泳回收。
将上述回收的pgc启动子片段和pgl3-basic片段连接,连接体系为t4buffer1μl,t4连接酶0.5μl,pgl3载体片段和pgc启动子片段以1:3比例补足10μl,混匀,16℃连接过夜。
将上述连接产物转化至trans1-t1phageresistant感受态细胞,具体操作如下:感受态细胞于冰上融化,向其中加入连接产物5μl,弹匀后冰浴30min;42℃水浴热击90s之后再冰浴2-3min;向感受态中加入1ml的无抗性的lb液体培养基,37℃摇床1h使菌体复苏;4000rpm离心2min,弃去800μl上清,然后吹打混匀剩余菌液;将剩余菌液涂布在含有氨苄青霉素抗性的lb固体培养基中,将菌板倒置于37℃培养箱中过夜培养。
挑选20个菌落进行菌液pcr验证,根据跑胶结果选取3个摇菌,提取质粒,进行测序验证,pcr结果见图2。
菌液pcr上游引物:5'-cgccactgcttctactga-3',下游引物:5'-cagacccgcatttgcaga-3'。
4.细胞转染
用omega去内毒素试剂盒提取重组质粒pgl3-pgc、阴性对照质粒pgl3-basic、阳性对照质粒pgl3-promoter及内对照质粒pgl3-tk。
将去内毒素提取的质粒转染ipec-j2细胞。具体操作如下:将阳性对照质粒pgl3-promoter、重组质粒pgl3-pgc和阴性对照质粒pgl3-basic分别与内对照质粒pgl3-tk按20:1混匀于150μl电击液中。
吸走6孔板中10%dmem,加1mlpbs冲洗一遍,加入500μl的胰酶消化细胞,待多数细胞变圆后,加入1ml10%dmem终止消化,吹打细胞并将细胞转移至15ml离心管中,1000g离心5min。尽可能将上清吸干净,用电击液和质粒的混液重悬细胞,转移至电击杯中;而后将电击杯放在核电转仪中,a024程序电击,程序结束后立即加入1ml10%dmem,重悬细胞,将其转移至24孔板,添加10%dmem至2ml,37℃培养。
5.双荧光素酶活性分析
转染24h后,吸走24孔板中10%dmem,pbs冲洗一遍;加入500μl的胰酶消化细胞,待多数细胞变圆后,加入1ml10%dmem终止消化,吹打细胞。每孔各吸取75μl细胞悬液至costar的96孔板,再向各孔加入75μldual-
虽然,上文中已经用一般性说明及具体实施方案对本发明作了详尽的描述,但在本发明基础上,可以对之作一些修改或改进,这对本领域技术人员而言是显而易见的。因此,在不偏离本发明精神的基础上所做的这些修改或改进,均属于本发明要求保护的范围。
序列表
<110>中国农业大学
<120>猪小肠上皮细胞表达的pgc启动子及其应用
<130>khp181119193.4
<160>5
<170>siposequencelisting1.0
<210>1
<211>3553
<212>dna
<213>2ambystomalateralexambystomajeffersonianum
<400>1
tgatgactgccacaggtgagggattggcagtggtggtgtgcgggctaatcacggccatct60
cttcttgaggcacggccagctgccagcattacttttttgtttgtttttttgttttgtttt120
gttttgtttttttagggcctcacctgcagcatatggacgttcccaagctaggggtccaat180
cggaggtacagccaccggcctacaccacagccacagcaatgcagaatccgagctgcgtct240
tcgacctataccacagctcacagcagtgccagatcctttacccactgagcaaggccaggg300
ctcacactggcaacctcatggttcttagtcggattcgtttctgctgctccaggatgggaa360
ctccgccagcatcacttctgtagtcactctgaaaggtgaatgggatgtttaaggggccgt420
gtgtgggaaaagatctcttttatttgctacaagtgataggatttgggtcaagccactggg480
atataaggtggtatggaataaataccgtaaggagaggaaaagcaaagttctccacaatag540
gggccagtttgagagcaggtgggcactgtagggaaggctctgtggcatctgtacaggggt600
cttgaaggatgagatcttgcaggtggagatgcttgagaagggtattgccgatgaaggaca660
cggcacggagcaaagtgtggaggctgggaaataactggcctcctggagagcaagaaaaag720
tcgccatggctggagcacagagccagtgtcagctcatagtagaagatgagcacggaattg780
taggagggggccagactgagtgtgtcctgatggccagagtgatgagtctggatctttttt840
acttaggctttgatgaggtgtgtgcgtgtatgtgtgtgtttatggctgctcctgcagcgt900
atggaagctcccaggctggcccacagccatgcgggatctgaactgcgtctgcgacctaca960
acacagcccatggcaacaccggatccttaacccactgagcaaggccagggatcgaacctg1020
catcctcatggatactagttgggttctaagcccctgagccacagtgggaactcctgccct1080
tgaatgacttcgaaggtgtcctcagactctcgctctaggaggagaggtcctgagggatgg1140
gctgaaccggacatgcagaaggaagagaaatgggctttccaggaatggggggctgggtcc1200
tggggggcggggggcagacaaggacttagaacttctgaggatcccaaggagacagacagg1260
ggctcagagccccagggcctgggagccaagcaggtggcctggctcaatgcagcaagccag1320
ggatactcagaagggatgtggtgtgactggggtttggggacagttagcccacagccatta1380
gacacctcgggttctgccagagaggccaaggcccatgttggggagtctggctggcctctt1440
aggggacttaggggaccccatggattctgctctattcataggatgtgattccaaggagag1500
ggtggctttcttttgcctgctctatcaaatctgtgattctcccaccccaaggatggcccc1560
cactcagtaccttgcctttcactccagagtccagcatgtccctggacacgacagggagga1620
atgggagctgacttggccttgagacccagtcaggcaggtacctccctctctgtgccaggc1680
ccgggcagacctctagtgccctccctctcctcctccctacaggctgggctggggggaggc1740
tccagggtgctggctgtgcagtgggtggcaggggccagagtggaaagtccccattggctg1800
gattacatcggcggttggcaggcctggtcttggccttctgcctggggctcaagggcctgg1860
gaaatctgtttggagccctgagtgaggggtacagggtggcagagagggtattggcctggg1920
gattttttccacttgccctaaaatggcgagttctcctatgccaggtgagtgggcgctagg1980
ccagctccaggtcacctcaggcaatgaggagcttgtagctggcaggcagggaggacctgg2040
gaatgaggaatggaggaggacacagcagatcaggcttgggatccgaagaagaggccgatg2100
agggccggggaagagggtgatggggaaggggcaggggctggggaagagggtagacacaca2160
ggggttttaggagaactaaagacgtgggcagagtcgcaatgagacagaagaagagagacg2220
tggaaaagcagcatcaggggcctgcacgtccccttgcccagccctcctgctgtcctagac2280
taatgccagaggcacacccagaagccagtagggtgttcccgctgtggtgcaatgggatcg2340
gtggcatcttgggagcgctgggacgcgggtttgatccctggccctggcacagtgggttaa2400
ggatctgatgttgctgcaacagtggctcgcatctgattcctggccgggggaactccctat2460
gccatggcgcagcccaaaaaagaaaagaaaccagtatgacttacgctgtgagcatgtcct2520
gagcatttgctgaattatgaagagaatttctccaaatgccccatctgaccaggaaaacct2580
cccaaacctccccccgccgcccagctctgacttgagccactggccacccagctccaccac2640
gtgcatccctgctgagaaaagagccatcgttaccaccatcagcaccacgctcactaccac2700
cgttatcgttaccctcatcctagctatggaccccccatcccctggacaccccacactgtg2760
tcccccaagggcttggaggtgctggagcctctgggtgcctcaccactataccagcgagtc2820
tcaacatttttgctcccaaaagggacattcggaaatgcctggagacgtgtggttgtcaca2880
gctgggggtgccgctggcatctaggggccagaggccagggatgcttttcaacctctggta2940
gaggcagcagagttatctgctgcacagtgtcagaagtcctgaggacagaaaaacctgccg3000
acagatcctactgtcctcactccgcccttctcgggccctcgccccaaagtgtccacctca3060
cacctctggttcctggacaagaagtcaacagggccctgctgcgttgggctctttgttctc3120
ttatcacttgcagctcctggccgccactgcttctactgaaaagtcaacatgatgaagagc3180
gctttgcggccgccctcacaggggaaaacacacagaaacaattgaggcccggagcccggg3240
gttcatcggggatggaggtcatgcttgtccagggcagggaggcggggcccgggctgcgtc3300
cccaggggtataaagcaggaaggagcgctcgggccttcactccacggcgacacacgacgt3360
agggtcacttctctgctgcggccagatgggcatgggcatcatgaagtggatggtgctggc3420
cttggtctgcctccaactcttggaggcgtcggttatcaagtgagtctggggcccggctgc3480
tggtctgcaaatgcgggtctgcaaggggcgacctgctgctgctctgggatttctagatta3540
gagcgataagcgg3553
<210>2
<211>28
<212>dna
<213>2ambystomalateralexambystomajeffersonianum
<400>2
cgacgcgttgatgtctgccacaggtgag28
<210>3
<211>30
<212>dna
<213>2ambystomalateralexambystomajeffersonianum
<400>3
ctagctagctgccgcttatcgctctaatct30
<210>4
<211>18
<212>dna
<213>2ambystomalateralexambystomajeffersonianum
<400>4
cgccactgcttctactga18
<210>5
<211>18
<212>dna
<213>2ambystomalateralexambystomajeffersonianum
<400>5
cagacccgcatttgcaga18
- 还没有人留言评论。精彩留言会获得点赞!