根尖牙乳头干细胞外泌体piRNA生物标志物及其筛选应用的制作方法
本发明属于生物医学技术领域,具体涉及一种根尖牙乳头干细胞外泌体pirna生物标志物及其筛选应用。
背景技术:
间充质干细胞(mesenchymalstemcells,mscs)是具有自我更新和多向分化潜能的祖细胞,具有多种生物学功能,尤其是在组织修复与再生中发挥重要作用。骨髓间充质干细胞(bonemarrowmesenchymalstemcells,bmmscs)是中胚层来源的干细胞,可作为种子细胞应用于组织工程、基因治疗和移植等领域。而根尖牙乳头干细胞(stemcellfromtheapicalpapilla,scap)是从人未发育成熟的恒牙根尖牙乳头中分离得到的一种外胚层神经嵴来源的间充质干细胞,与bmmscs相比较具有更高的增殖、迁移、分化和免疫调节能力,并且来源丰富,不存在伦理及法律上的争议,是组织工程中理想的种子细胞来源。目前这两种干细胞尚没有统一的评价其生物学功能特性的方法。
外泌体是细胞分泌的微囊泡,直径为30-150nm,包被细胞的双层脂膜结构。外泌体是介导细胞之间相互交流的一种重要方式。外泌体中含有多种活性成分,包括脂质、蛋白质、rna和dna等,特别是外泌体中所包含的rna,被认为是调控受体细胞的主要物质。mscs来源的外泌体与mscs有着相似的功能,包括促进组织修复与再生、抑制炎症反应及调节机体免疫等。
pirna(piwi-interactingrna)是近年来发现的一类新型小非编码rna,通过与piwi家族蛋白结合调控靶基因和转座子的活性。pirna在维持干细胞基因组稳定和哺乳动物精子生成过程中发挥重要作用,与干细胞功能紧密相关。
技术实现要素:
本发明的目的是评价根尖牙乳头干细胞和骨髓间充质干细胞的生物学功能,探讨其在再生医学领域的应用,提供一种根尖牙乳头干细胞外泌体pirna生物标志物及其筛选应用,涉及干细胞与再生医学、分子生物学和转录组学,尤其涉及应用二代测序技术分析根尖牙乳头干细胞和骨髓间充质干细胞外泌体中pirna表达谱的方法,并将该方法用于评价干细胞功能特性,具体获得了scap和bmmscs两种间充质干细胞外泌体的pirna测序数据,并对差异表达的pirna靶基因进行功能富集和信号通路分析。结合文献计量学,通过资料查询及大量文献检索,将本评价方法和已有的研究结果对比分析,为评价根尖牙乳头干细胞和骨髓间充质干细胞功能特性和应用提供新的方法和技术手段。
为实现上述目的,本发明采用以下技术方案:
根尖牙乳头干细胞外泌体pirna生物标志物,如seqidno.1~21所示,包括:hsa_pir_001168,hsa_pir_020326,hsa_pir_017724,hsa_pir_002332,hsa_pir_011273,hsa_pir_019521,hsa_pir_020793,hsa_pir_020388,hsa_pir_019949,hsa_pir_017716,hsa_pir_016946,hsa_pir_001184,hsa_pir_014620,hsa_pir_001788,hsa_pir_012895,hsa_pir_002811,hsa_pir_020829,hsa_pir_008803,hsa_pir_019912,hsa_pir_007832,hsa_pir_015026。
所述的根尖牙乳头干细胞外泌体pirna生物标志物的筛选方法,包括以下步骤:
(1)间充质干细胞上清液的收集:
分别对根尖牙乳头干细胞scap和骨髓间充质干细胞bmmscs进行培养,使各自细胞融合度达到80%后,在去外泌体血清培养基中,连续培养48h后,分别收集scap培养基上清液和bmmscs培养基上清液;
(2)外泌体提取:
对步骤(1)收集的间充质干细胞培养基上清液,分别相应进行外泌体提取操作;
(3)总rna提取:
将步骤(2)收集的外泌体,分别相应进行各自总rna提取操作;
(4)srna文库的建立及测序:
对步骤(3)获取的总rna分别相应进行pcr扩增,构建各自的srna文库,并进行高通量并行测序;
(5)测序结果的处理和注释:
对步骤(4)测序后获得序列初步过滤,得到干净序列;各自分别与rfam和pirna数据库比对,将两数据库重复所得srna分类注释结果进行统计,鉴定scap外泌体和bmmsc外泌体中含有pirna,并记录各自pirna的表达结果;
(6)两样本pirna比对进行表达差异分析:
根据(5)统计得到的scap外泌体和bmmscs外泌体中pirna的表达结果比对,进行差异分析,差异标准为|log2(foldchange)|>1;p<0.05,筛选出差异表达的pirna,共21个,其中包括seqidno.1~15为15个上调pirna,seqidno.16~21为6个下调pirna,即为生物标志物,并记录差异表达结果。
所述的步骤(1)中,scap经提取获得,提取过程为:取未发育完成的年轻恒牙,提取根尖牙乳头,经分离,获得根尖牙乳头干细胞。
所述的步骤(1)中,bmmscs来自市购。
所述的步骤(2)中,采用exoquick-tctm试剂盒对上清液进行外泌体提取操作。
所述的步骤(3)中,采用trizol试剂对提取到的外泌体进行总rna提取操作。
所述的根尖牙乳头干细胞外泌体pirna生物标志物作为scap特异性的鉴别诊断标志物的应用。
所述的根尖牙乳头干细胞外泌体pirna生物标志物在制备用于评价组织再生能力试剂盒中的应用。
所述的根尖牙乳头干细胞外泌体pirna生物标志物在制备相应pirna的抑制剂及其在骨再生和血管生成中的应用。
所述的根尖牙乳头干细胞外泌体pirna生物标志物在制备相应pirna的模拟物及其在神经再生和血管再生中的应用。
对差异表达的pirna进行靶基因预测,获得差异表达pirna的靶基因,然后对差异表达pirna的靶基因进行go/kegg功能富集分析,获得分析结果,具体的利用本方法评价干细胞功能特性和现有文献比对研究:
对功能富集的pathway同美国国家医学图书馆下属的国家生物技术信息中心开发的数据库pubmed中现有文献比对,进一步评估本方法在评价scap及bmmscs生物学功能特性方面的可行性。
二代测序技术具有极高的测序速度和高度准确性,能够达到测序成本低、通量高,具有大规模应用的潜能。因此,本实验应用二代测序技术分析根尖牙乳头干细胞和骨髓间充质干细胞外泌体中pirna表达谱,以及对差异表达的pirna靶基因功能进行分析,对研究根尖牙乳头干细胞和骨髓间充质干细胞生物学功能与特性具有重要意义。
本发明的有益效果:
本发明通过高通量测序技术建立小rna数据库,具有分辨率高、精确度高,重复性高且成本低的优势,可全面获取scap和bmmscs两种间充质干细胞外泌体中pirna的表达信息。根据scap和bmmscs外泌体中pirna的表达信息,分析pirna差异表达结果,对表达的pirna进行靶基因预测和靶基因go/kegg功能富集分析,深入研究差异表达的pirna功能。pirna是一种可调控基因表达的非编码rna,对外泌体中pirna功能的深度挖掘,有助于进一步研究根尖牙乳头干细胞和骨髓间充质干细胞的生物学功能,并提供可靠数据和新的思路。
附图说明:
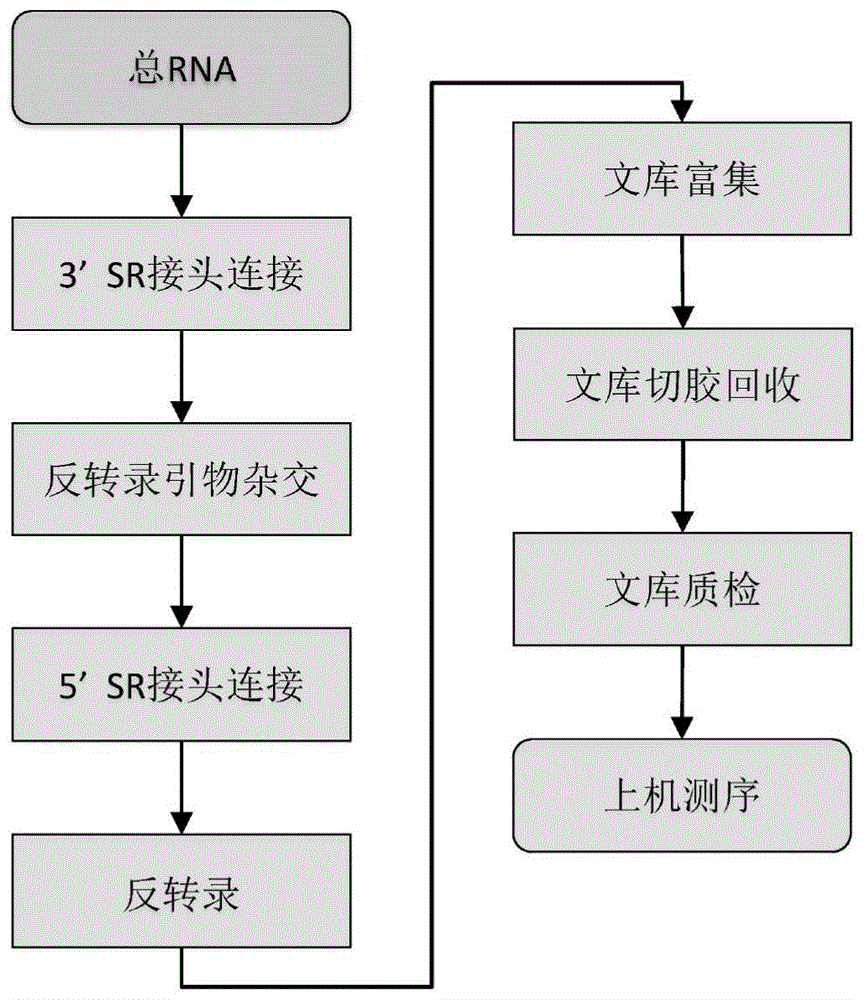
图1为二代测序技术路线图;
图2为scap中srna分类注释百分比图;
图3为bmmscs中srna分类注释百分比图;
图4为高通量测序差异表达pirna的热图;
图5为scapv.sbmmscs上调差异表达pirna靶基因的go富集结果图;
图6为scapv.sbmmscs下调差异表达pirna靶基因的go富集结果图;
图7为scapv.sbmmscs上调差异表达pirna靶基因的kegg富集结果图;
图8为scapv.sbmmscs下调差异表达pirna靶基因的kegg富集结果图;
图9为scapv.sbmmscs上调差异表达pirna靶基因富集pathway相关文献统计结果图;
图10为scapv.sbmmscs下调差异表达pirna靶基因富集pathway相关文献统计结果图。
具体实施方式:
下面结合实施例对本发明作进一步的详细说明。
以下实施例的骨髓间充质干细胞来源于市购,srna即为小rna,smallrna,采用的二代测序技术路线图如图1所示。
实施例1
根尖牙乳头干细胞外泌体pirna生物标志物,如seqidno.1~21所示,包括:hsa_pir_001168,hsa_pir_020326,hsa_pir_017724,hsa_pir_002332,hsa_pir_011273,hsa_pir_019521,hsa_pir_020793,hsa_pir_020388,hsa_pir_019949,hsa_pir_017716,hsa_pir_016946,hsa_pir_001184,hsa_pir_014620,hsa_pir_001788,hsa_pir_012895,hsa_pir_002811,hsa_pir_020829,hsa_pir_008803,hsa_pir_019912,hsa_pir_007832,hsa_pir_015026。
所述的根尖牙乳头干细胞外泌体pirna生物标志物的筛选方法,包括以下步骤:
1、间充质干细胞上清液的收集:
scap、bmmscs常规培养,在细胞融合度达到80%时,更换去外泌体血清培养基连续培养48h后收集上清液。
2、外泌体提取:
将收集的间充质干细胞培养基上清液按以下步骤提取外泌体:
(1)取10ml上清液以3,000×g、4℃,离心15min去除细胞碎片;
(2)将去除细胞碎片后的上清液到新的15ml离心管中,不碰触沉淀,放于冰上。加入2mlexoquick-tcexosomeprecipitationsolution,放置冰上,上下颠倒混匀,获得混合物;
(3)冷藏过夜(至少12h),孵育期间静置;
(4)1500×g、4℃、30min离心混合物,离心结束后,获得白色或米白色沉淀物;
(5)弃去上清,再以1500×g、4℃离心5min以除去exoquick-tcsolution残余,获得外泌体沉淀;
(6)100-500μl的buffer重悬外泌体沉淀物,透射电镜观察外泌体。-80℃保存。
3、总rna提取:
(1)取富集的外泌体50μl,加入1.0mltrizol试剂,吹打混匀,冰上静置5min,使得核酸蛋白复合物完全分离;
(2)加氯仿0.2ml,漩涡震荡30s,冰上静置10min;
(3)12000rpm、15min、4℃离心。然后取上层无色水相(约0.6ml)到离心管,加等体积异丙醇,冰上静置10min;
(4)12000rpm、15min、4℃离心,管底获得淡黄色沉淀,弃去上清,加入75%乙醇1.0ml,漩涡震荡30s,洗涤,12000rpm、10min、4℃离心;
(5)用75%乙醇重复洗一次。弃上清,离心30s,用移液枪吸去残余液体,室温,晾干(离心管壁上无水珠为宜),加入25μldepc水,进行洗脱,完成提取,获得总rna;
(6)将提取的总rna立即-80℃保存;
4、srna文库的建立及illumina测序:
采用的二代测序技术,先对提取的总rna进行3′端和5′端连接修饰,在反转录酶作用下,以rtprimer为引物进行反转录,进行pcr扩增,生成稳定易用的文库用于测序。使用聚丙烯酰胺凝胶电泳回收150bp的文库,并吸取1μl文库于qubitfluorometer(invitrogen,美国)检测文库浓度,大于1.0ng/l即为合格文库,形成srna文库。
将srna文库混合、变性后,加入到illuminahiseqxten测序平台进行高通量并行测序。
5、测序结果的处理和注释:
illuminahiseqxten测序所得序列,通过去接头和去掉低质量序列等过程,完成原始数据的初步过滤,得到干净序列;将获得的干净序列与rfam和pirna数据库比对,获得样本中srna分类与注释结果,分类统计,scap中srna分类注释百分比图如图2所示,由图2可知,pirna为12.45%,othersrna为10.11%,rrna15.53%,snrna6.25%,trna4.58%,unknown为51.09%;bmmscs中srna分类注释百分比图如图3所示,由图3可知,pirna为7.06%,othersrna为10.84%,rrna14.60%,snrna8.90%,trna2.74%,unknown为55.85%;鉴定scap外泌体和bmmscs外泌体中含有pirna,并记录各pirna的表达结果。
6、样本pirna表达差异分析:
根据(5)统计得到的scap外泌体和bmmscs外泌体中pirna的表达结果,根据pirna在各样本表达量使用deseq2(version1.20.0)软件进行差异分析,差异标准为|log2(foldchange)|>1;p<0.05,筛选出差异表达的pirna,并记录差异表达结果,即为生物标志物,pirna差异表达结果如下表1所示,高通量测序获得的差异表达pirna热图如图4所示;
表1pirna差异表达结果
scapv.sbmmscs(up):scap外泌体与bmmscs外泌体相比,表达量呈上调趋势的pirna,即scap外泌体表达量高于bmmscs外泌体的pirna;
scapv.sbmmscs(down):scap外泌体与bmmscs外泌体相比,表达量呈下调趋势的pirna,即scap外泌体表达量低于bmmscs外泌体的pirna。
7、靶基因预测及功能分析:
对差异表达的pirna使用miranda(v3.3a)和rnahybrid进行靶基因预测。然后对靶基因进行go分类和keggpathway的功能分析,进行显著性基因功能筛选,scapv.sbmmscs上调差异表达pirna靶基因的go富集结果图如图5所示,scapv.sbmmscs下调差异表达pirna靶基因的go富集结果图如图6所示,scapv.sbmmscs上调差异表达pirna靶基因的kegg富集结果图如图7所示,scapv.sbmmscs下调差异表达pirna靶基因的kegg富集结果图如图8所示,scapv.sbmmscs上调差异表达pirna靶基因富集pathway相关文献统计结果图如图9所示,scapv.sbmmscs下调差异表达pirna靶基因富集pathway相关文献统计结果图如图10所示。
8、利用本方法进行功能分析获得结果和现有文献比对研究:
将scapv.sbmmscs(up)组功能富集的pathway同美国国家医学图书馆下属的国家生物技术信息中心开发的数据库pubmed中scap功能报道文献比对,将scapv.sbmmscs(down)组功能富集的pathway同bmmscs功能报道文献比对,进一步评估本方法在评价bmmscs及scap生物学功能特性方面的可行性。
结果:
scap外泌体与bmmscs外泌体相比,差异表达的pirna共21个(表1),呈上调趋势的pirna为15个,可能参与代谢、细胞生长、分化、凋亡等生理过程、心肌收缩功能和疾病等相关通路;呈下调趋势的pirna为6个,可能参与代谢、细胞凋亡、肿瘤发生和eb病毒感染等相关通路。
经文献证实的骨髓间充质干细胞功能与用本方法评价相一致的文献量统计如下:“lysosome信号通路”相关文献15篇、“aminoacyl-trnabiosynthesis信号通路”相关文献1篇、“cysteineandmethioninemetabolism信号通路”相关文献7篇、“fattyacidmetabolism信号通路”相关文献642篇、“epstein-barrvirusinfection信号通路”相关文献16篇、“apoptosis信号通路”相关文献807篇、“biosynthesisofunsaturatedfattyacids信号通路”相关文献274篇、“pyruvatemetabolism信号通路”相关文献28篇、“p53信号通路”相关文献232篇,与细胞增殖、自噬、血管生成、氨基酸和脂质代谢和骨再生等功能相关。
查询到关于骨髓间充质干细胞外泌体功能文献共66篇,其中涉及到8条信号通路,和本方法评价一致的通路有2条,为apoptosis信号通路和p53信号通路,与细胞自噬和细胞增殖相关。表明用本方法评价骨髓间充质干细胞及其外泌体功能是确实有效的。
目前关于根尖牙乳头干细胞功能报道文献尚少,共37篇,经文献证实的根尖牙乳头干细胞功能与本方法评价相一致的文献量为:“mapk信号通路”相关文献6篇、“calcium信号通路”相关文献4篇。主要与骨组织生成和牙齿组织的生长发育相关。本方法评价根尖牙乳头干细胞功能高表达pirna功能与糖类、脂类、氨基酸和碳代谢通路相关,这符合此前报道干细胞在机体新陈代谢中起重要作用,并且三羧酸循环是机体代谢过程中获取能量的主要方式,mapk信号通路调控细胞的增殖和分化等生理过程,这些通路都与牙齿的发育和骨组织的形成紧密相关。
综上所述,本方法通过干细胞外泌体pirna测序评价干细胞生物学功能,可有效评价间充质干细胞功能。获得的根尖牙乳头干细胞外泌体pirna生物标志物可以作为scap特异性的鉴别诊断标志物进行应用;包括应用其制备用于评价组织再生能力的试剂盒;以及相应pirna的抑制剂及其在骨再生和血管生成中的应用、相应pirna的模拟物及其在神经再生和血管再生的制备。对根尖牙乳头干细胞功能评价及其在再生医学的应用研究,可为后续根尖牙乳头干细胞功能验证具有良好的提示作用。
序列表
<110>中国医科大学附属口腔医院
<120>根尖牙乳头干细胞外泌体pirna生物标志物及其筛选应用
<141>2019-03-18
<160>21
<170>siposequencelisting1.0
<210>1
<211>22
<212>rna
<213>unknown
<400>1
aggguuuacgaccucgauguug22
<210>2
<211>26
<212>rna
<213>unknown
<400>2
uggugguucagugguagaauucucgc26
<210>3
<211>21
<212>rna
<213>unknown
<400>3
guagugguuaucacguucgcc21
<210>4
<211>25
<212>rna
<213>unknown
<400>4
aguccgacgaucagagggacggccg25
<210>5
<211>26
<212>rna
<213>unknown
<400>5
aaaagcccugaacucagaagugauua26
<210>6
<211>24
<212>rna
<213>unknown
<400>6
gugcuuaguugaacagggcccuga24
<210>7
<211>21
<212>rna
<213>unknown
<400>7
cgcgguuagcucagugguaga21
<210>8
<211>21
<212>rna
<213>unknown
<400>8
gcguguggucuagggguaugg21
<210>9
<211>25
<212>rna
<213>unknown
<400>9
gcccggauagcucaguugguagagc25
<210>10
<211>17
<212>rna
<213>unknown
<400>10
uagugguuaggauucgg17
<210>11
<211>25
<212>rna
<213>unknown
<400>11
uucggcuguuaaccgaaagguuggu25
<210>12
<211>22
<212>rna
<213>unknown
<400>12
gaaaagguguugguugauauag22
<210>13
<211>23
<212>rna
<213>unknown
<400>13
aucauuggucgugguuguagucc23
<210>14
<211>20
<212>rna
<213>unknown
<400>14
ccuucgggcgagguucaccg20
<210>15
<211>20
<212>rna
<213>unknown
<400>15
ugcuggcaacagugucuggu20
<210>16
<211>20
<212>rna
<213>unknown
<400>16
cuuuguagggacacggauga20
<210>17
<211>16
<212>rna
<213>unknown
<400>17
uuccguaguguagugg16
<210>18
<211>21
<212>rna
<213>unknown
<400>18
ccauuaccaugcuguuuuggu21
<210>19
<211>23
<212>rna
<213>unknown
<400>19
cggaugauccucaguggucuggg23
<210>20
<211>20
<212>rna
<213>unknown
<400>20
gcaguggcgcgaucucggcu20
<210>21
<211>26
<212>rna
<213>unknown
<400>21
gguucagugguagaauucucgccucc26
- 还没有人留言评论。精彩留言会获得点赞!