一种用于监测IgA肾病的生物标志物的制作方法
本发明属于医学检测领域,涉及一种用于监测iga肾病的生物标志物。
背景技术:
iga肾病(iganephropathy,igan)是世界上最常见的原发性血管球性肾炎。尽管总体人群中igan的患病率较低,但其流行率很高,特别是在亚洲,在肾活检中估计为30-40%。大约30-40%的igan患者将进展至结束-(ersd)在20-30年内,使igan成为全球ersd的主要原因。然而,目前关于igan的发病机制仍不清楚,可用的治疗只能缓解症状并延缓需要透析和肾移植。在igan患者中,一些患者治疗效果良好且可以长时间维持肾功能,然而不太明白的是,有一些患者对治疗有抵抗并需要透析更迅速,并且igan患者的死亡率甚至比开始透析治疗前更高(knoopetal.2013),这也与早期透析治疗可能是有益的观点相悖。目前,透析主要根据血清肌酐水平(>500mg/dl)和egfr(<15ml/min)水平进行介入治疗。缺乏适当的生物标志物来监测igan的状态和进展使得难以判断何时需要进行透析。此外,目前用于评估igan状态的两种主要标志物,即血清肌酸酐和蛋白尿,但肾小球和肾小管间质的损伤检测准更为准确。肾活检是侵入性的,并可能导致并发症,并不适合监测病情进展。因此,目前急需找到合适的标志物,既可预测igan患者结果又能监测疾病进展。
参考文献
knoop,t.etal.,2013.mortalityinpatientswithiganephropathy.americanjournalofkidneydiseases:theofficialjournalofthenationalkidneyfoundation,62(5),pp.883–890.获取自网址:http://linkinghub.elsevier.com/retrieve/pii/s0272638613008226.
技术实现要素:
mirna是在各种组织和体液中发现的小的非编码rna分子,在通过转录后调节基因表达来维持肾体内稳态中起重要作用。它们也在慢性肾脏疾病中发挥重要作用,如高血压性肾病和糖尿病肾小球硬化症。然而,目前有关mirna在igan中的具体作用的研究报道仍然较少。因此,microrna可能参与了igan的进展,可能被用作生物标志物来监测igan疾病并预测患者结果。为此,本发明选择了19种可能在肾脏中发挥作用的microrna功能和测量它们的血浆水平在尚未接受治疗的igan患者中。本发明发现与健康受试者相比,13个微rna中的13个显示改变的血浆水平。本发明进一步分析了这13种microrna对治疗的反应,以探索其作为生物标志物的潜力。本发明发现mir-29a,mir-141,mir-200a,mir-204,mir-205和mir-429显示出显着改变治疗前和治疗后的血浆水平,表明这些microrna可能反映疾病的状态并用作生物标志物。然后本发明分析它们的水平是否与igan患者接受治疗有关。本发明发现该类患者中血浆mir-29a和mir-205与血清肌酐、gfr以及蛋白尿相关。此外,mir-29a的下调和mir-205的上调,可能作为预测igan的进展的标志物,即具有低血浆水平的mir-29a或高血浆mir-205水平的患者可能意味着进展到igan的晚期阶段。本发明的研究表明mir-29a和mir-205可以用作生物标志物来监测igan的进展并且可以提供比血清肌酸酐、egfr更多的指标来评估igan患者是否应该进行透析治疗。
为了解决现有技术的不足,本发明提供了一种用于监测或检测iga肾病发病过程和/或治疗过程的小rna类生物标记物,所述生物标记物选自mir-15a,mir-16,mir-21,mir-29a,mir-34a,mir-125b,mir-141,mir-148b,mir-155,mir-184,mir-192,mir-200a,mir-200b,mir-200c,mir-204,mir-205,mir-210,mir-301a,和mir-429中的任一种、任两种、任三种、任四种、任五种、任六种、任七种、任八种、任九种、任十种、任十一种、任十二种、任十三种、任十四种、任十五种、任十六种、任十七种、任十八种或十九种。
在一些事实方式中,所述生物标记物为mir-29a和/或mir-205。
在一些事实方式中,针对mir-15a,
其核酸序列为:uagcagcacauaaugguuugug,其序列如seqidno.1所示;
针对mir-16,
其核酸序列为:uagcagcacguaaauauuggcg,其序列如seqidno.2所示;
针对mir-21,
其核酸序列为:uagcuuaucagacugauguuga,其序列如seqidno.3所示;
针对mir-29a,
其核酸序列为:uagcaccaucugaaaucgguua,其序列如seqidno.4所示;
针对mir-34a,
其核酸序列为:uggcagugucuuagcugguugu,其序列如seqidno.5所示;
针对mir-125b,
其核酸序列为:ucccugagacccuaacuuguga,其序列如seqidno.6所示;
针对mir-141,
其核酸序列为:
cggccggccctgggtccatcttccagtacagtgttggatggtctaattgtgaagctcctaacactgtctggtaaagatggctcccgggtgggttc,其序列如seqidno.7所示;
针对mir-148b,
其核酸序列为:ucagugcaucacagaacuuugu,其序列如seqidno.8所示;
针对mir-155,
其核酸序列为:uuaaugcuaaucgugauaggggu,其序列如seqidno.9所示;
针对mir-184,
其核酸序列为:uggacggagaacugauaagggu,其序列如seqidno.10所示;
针对mir-192,
其核酸序列为:cugaccuaugaauugacagcc,其序列如seqidno.11所示;
针对mir-200a,
其核酸序列为:uaacacugucugguaacgaugu,其序列如seqidno.12所示;
针对mir-200b,
其核酸序列为:uaauacugccugguaaugauga,其序列如seqidno.13所示;
针对mir-200c,
其核酸序列为:uaauacugccggguaaugaugga,其序列如seqidno.14所示;
针对mir-204,
其核酸序列为:uucccuuugucauccuaugccu,其序列如seqidno.15所示;
针对mir-205,
其核酸序列为:uccuucauuccaccggagucug,其序列如seqidno.16所示;
针对mir-210,
其核酸序列为:cugugcgugugacagcggcuga,其序列如seqidno.17所示;
针对mir-301a,
其核酸序列为:cagugcaauaguauugucaaagc,其序列如seqidno.18所示;以及
针对mir-429,
其核酸序列为:uaauacugucugguaaaaccgu,其序列如seqidno.19所示。
在一些事实方式中,所述生物标记物来自血浆。
在一些事实方式中,所述生物标记物mir-29a为血浆mir-29a,和/或所述生物标记物mir-205为血浆mir-205。
在一些事实方式中,所述治疗过程包括向患有iga肾病的患者施用缬沙坦,或联合施用霉酚酸酯与强的松。
在一些事实方式中,所述施用缬沙坦的治疗方案为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2的病人,每人每日80mg,若出现低血压不能耐受或肌酐进行性升高,减量或停用;
所述联合施用霉酚酸酯与强的松的治疗方案为:针对尿蛋白>1g/24小时,egfr>30ml/min/1.73m2,病理新月体占10-50%的病人,霉酚酸酯剂量1g至1.5g每天,强的松0.5mg每公斤体重每天,分别分两次口服,维持治疗半年后减量,疗程1年半。
这些标记物能够用于良好地检测治疗过程。
附图说明
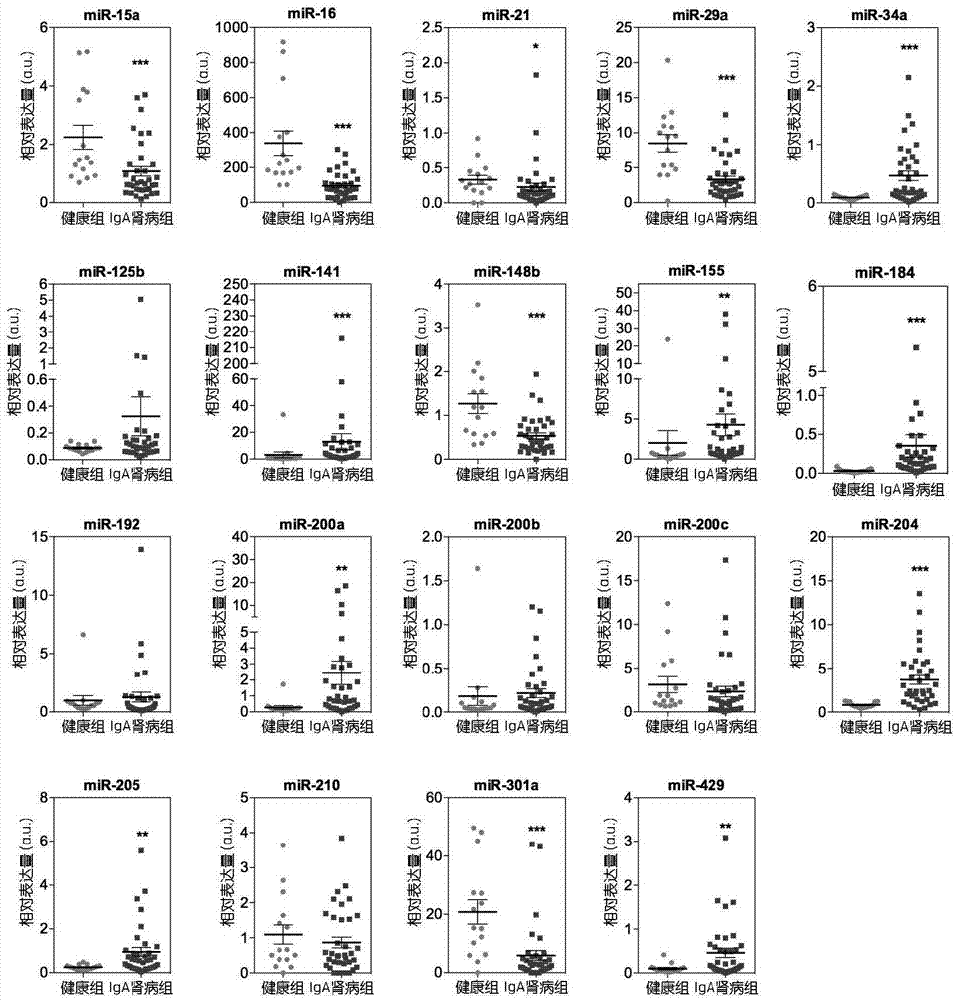
图1示出了iga肾病病人的血浆microrna水平的改变情况。
图2示出了经治疗后的iga肾病病人血浆microrna水平的回调情况。
图3示出了经治疗后的iga肾病病人某些血浆microrna水平的变化情况。
图4示出了血浆mir-29a水平与肾小球透过率和蛋白尿的关联性。
图5示出了血浆mir-205水平与肾小球透过率和蛋白尿的关联性。
图6示出了血浆mir-29a和mir-205水平与尿液水平的相关性。
图7示出了尿液mir-29a水平与肾小球透过率、蛋白尿和血清肌酐的相关性。
图8示出了尿液mir-205水平与肾小球透过率、蛋白尿和血清肌酐的相关性。
图9示出了血浆mir-29a和mir-205水平与iga肾病病程的预测的相关性。
具体实施方式
为了更好的解释本发明的技术方案,下面结合附图详细介绍本发明的实施例。以下实施例用于进一步说明本发明,但不应理解为对本发明的固定或限制。若未特别指明,实施例中所用的技术特征可以替换为具有在不背离发明构思前提下等同或相似功能或效果的其他本领域已知的技术特征。
1.试验
1.1.样品采集
在这项研究中,招募了15名健康受试者和36名未经治疗的肾活检证实的igan患者,年龄和性别分布相似(表1)。当时收集血液和尿液样本进行肾活检。相比健康受试者,未治疗的igan患者血清肌酐水平显著高,蛋白尿(bloodureanitrogen,bun)低,egfr(肾小球滤过率)低(表1)。
表1健康组与未治疗的iga肾病病人的基础临床数据
数据以平均值±sem显示;&;p<0.01。mann-whitney测试(onetail)
从这些患者中,有19名患者决定接受在深圳大学第一附属医院治疗,治疗方案如下:
施用血管紧张素受体阻滞剂(arbs)缬沙坦的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2的病人,每人每日80mg,若出现低血压不能耐受或肌酐进行性升高,减量或停用。
施用霉酚酸酯(mmf)的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2,病理新月体占10-50%的病人。剂量1g至1.5g每天,分两次口服,维持治疗半年后减量,疗程1年半。使用mmf联合强的松,mmf不单用。
施用强的松的步骤为:强的松0.5mg每公斤体重每天,半年后逐步减量,疗程1年半。
联合使用的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2,病理新月体占10-50%的病人。施用霉酚酸酯剂量1g至1.5g每天,分两次口服,强的松0.5mg每公斤体重每天,维持治疗半年后减量,疗程1年半。
并用霉酚酸酯(mmf)和强的松联合使用持续3个月。
期间收集了血液和尿液样本。治疗后,igan患者显示血清肌酐水平和蛋白尿降低,egfr增加(表2)。
表2iga肾病病人治疗前后临床数据对比
女性(n=12,平均年龄:40.25±3.17);男性(n=7,平均年龄:32.86±2.53);平均年龄:37.53±2.32。
为了揭示血浆和尿微小rna之间的关系和疾病的进展关系,本发明研究了79例肾活检正在接受上述方案治疗的igan患者。平均而言,血浆和尿液样本是患者接受治疗的一年的期间收集完成的。知情同意书已与每个患者和健康的受试者签订。本研究经深圳大学第一附属医院伦理委员会批准。
1.2.样品处理
从前述79例受试者各收集5毫升全血,并在4℃下暂时保存全血少于3小时然后在4℃下以3000xg离心30分钟。离心后,收集,等分并在-80℃下储存血浆直到使用。用含有rnase抑制剂(am2696,thermofisher)的塑料瓶收集二十四小时的尿。然后将混合的尿液样品在4℃下以12,000xg离心10分钟以去除任何碎片。等分的尿液样品储存在-80℃下直到使用。避免重复冻融血浆和尿样。
1.3.mirna分离和逆转录
使用mirvanaparis试剂盒分别从血浆和尿液中提取包括小rna的总rna(ambion,fostercity,ca,usa)遵循制造商提供的使用说明书。使用nanodrop分光光度计(nanodroptechnologies,wilmington,de)对rna浓度进行定量测定和1μg总rna按照制造商的标准使用miscriptreversetranscriptionkit(qiagen)进行反转录流程。
针对mir-15a,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcacaaa,其序列如seqidno.58所示;
针对mir-16,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcgccaa,其序列如seqidno.59所示;
针对mir-21,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcaacat,其序列如seqidno.60所示;
针对mir-29a,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaaccga,其序列如seqidno.61所示;
针对mir-34a,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacaacc,其序列如seqidno.62所示;
针对mir-125b,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcacaag,其序列如seqidno.63所示;
针对mir-141,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttccatct,其序列如seqidno.64所示;
针对mir-148b,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacaaag,其序列如seqidno.65所示;
针对mir-155,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacccct,其序列如seqidno.66所示;
针对mir-184,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaccctt,其序列如seqidno.67所示;
针对mir-192,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttggctgt,其序列如seqidno.68所示;
针对mir-200a,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacatcg,其序列如seqidno.69所示;
针对mir-200b,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcatcat,其序列如seqidno.70所示;
针对mir-200c,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttccatca,其序列如seqidno.71所示;
针对mir-204,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaggcat,其序列如seqidno.72所示;
针对mir-205,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcagact,其序列如seqidno.73所示;
针对mir-210,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcagccg,其序列如seqidno.74所示;
针对mir-301a,
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttgctttg,其序列如seqidno.75所示;
针对mir-429
逆转录所用引物为:
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacggtt,其序列如seqidno.76所示。
1.4.定量rt-pcr
实时rt-pcr用于定量mirna的一个子集(mir-15a,mir-16,mir-21,mir-29a,mir-34a,mir-125b,mir-141,mir-148b,mir-155,mir-184,mir-192,mir-200a,mir-200b,mir-200c,mir-204,mir-205,mir-210,mir-301a,mir-429,加上内源性对照),用miscript进行primerassays和qiagen公司的miscriptsybrgreenpcr试剂盒。实时pcr扩增反应是在icycler(bio-rad)上通过sybrgreen化学以25μl终体积重复三次进行。使用内部对照,cel-mir-54进行标准化。比较实时pcr是一式三份,包括无模板控件。
针对mir-15a,
其核酸序列为:uagcagcacauaaugguuugug,其序列如seqidno.1所示;
确定丰度所用pcr引物为:
f:ccgggtagcagcacataatgg,其序列如seqidno.20所示;
r:gtgcagggtccgaggt,其序列如seqidno.21所示;
针对mir-16,
其核酸序列为:uagcagcacguaaauauuggcg,其序列如seqidno.2所示;
确定丰度所用pcr引物为:
f:ttcggtagcagcacgtaaata,其序列如seqidno.22所示;
r:gtgcagggtccgaggt,其序列如seqidno.23所示;
针对mir-21,
其核酸序列为:uagcuuaucagacugauguuga,其序列如seqidno.3所示;
确定丰度所用pcr引物为:
f:ttcggtagcttatcagactga,其序列如seqidno.24所示;
r:gtgcagggtccgaggt,其序列如seqidno.25所示;
针对mir-29a,
其核酸序列为:uagcaccaucugaaaucgguua,其序列如seqidno.4所示;
确定丰度所用pcr引物为:
f:ttcggtagcaccatctgaaat,其序列如seqidno.26所示;
r:gtgcagggtccgaggt,其序列如seqidno.27所示;
针对mir-34a,
其核酸序列为:uggcagugucuuagcugguugu,其序列如seqidno.5所示;
确定丰度所用pcr引物为:
f:cggtggcagtgtcttagct,其序列如seqidno.28所示;
r:gtgcagggtccgaggt,其序列如seqidno.29所示;
针对mir-125b,
其核酸序列为:ucccugagacccuaacuuguga,其序列如seqidno.6所示;
确定丰度所用pcr引物为:
f:tggtccctgagaccctaac,其序列如seqidno.30所示;
r:gtgcagggtccgaggt,其序列如seqidno.31所示;
针对mir-141,
其核酸序列为:
cggccggcccuggguccaucuuccaguacaguguuggauggucuaauugugaagcuccuaacacugucugguaaagauggcucccggguggguuc,其序列如seqidno.7所示;
确定丰度所用pcr引物为:
f:ttcggtaacactgtctggtaa,其序列如seqidno.32所示;
r:gtgcagggtccgaggt,其序列如seqidno.33所示;
针对mir-148b,
其核酸序列为:ucagugcaucacagaacuuugu,其序列如seqidno.8所示;
确定丰度所用pcr引物为:
f:tcggtcagtgcatcacagaa,其序列如seqidno.34所示;
r:gtgcagggtccgaggt,其序列如seqidno.35所示;
针对mir-155,
其核酸序列为:uuaaugcuaaucgugauaggggu,其序列如seqidno.9所示;
确定丰度所用pcr引物为:
f:ttcggttaatgctaatcgtgat,其序列如seqidno.36所示;
r:gtgcagggtccgaggt,其序列如seqidno.37所示;
针对mir-184,
其核酸序列为:uggacggagaacugauaagggu,其序列如seqidno.10所示;
确定丰度所用pcr引物为:
f:cggtggacggagaactgat,其序列如seqidno.38所示;
r:gtgcagggtccgaggt,其序列如seqidno.39所示;
针对mir-192,
其核酸序列为:cugaccuaugaauugacagcc,其序列如seqidno.11所示;
确定丰度所用pcr引物为:
f:gtcggctgacctatgaattg,其序列如seqidno.40所示;
r:gtgcagggtccgaggt,其序列如seqidno.41所示;
针对mir-200a,
其核酸序列为:uaacacugucugguaacgaugu,其序列如seqidno.12所示;
确定丰度所用pcr引物为:
f:ttcggtaacactgtctggtaa,其序列如seqidno.42所示;
r:gtgcagggtccgaggt,其序列如seqidno.43所示;
针对mir-200b,
其核酸序列为:uaauacugccugguaaugauga,其序列如seqidno.13所示;
确定丰度所用pcr引物为:
f:ttcggtaatactgcctggtaa,其序列如seqidno.44所示;
r:gtgcagggtccgaggt,其序列如seqidno.45所示;
针对mir-200c,
其核酸序列为:uaauacugccggguaaugaugga,其序列如seqidno.14所示;
确定丰度所用pcr引物为:
f:cggtaatactgccgggtaat,其序列如seqidno.46所示;
r:gtgcagggtccgaggt,其序列如seqidno.47所示;
针对mir-204,
其核酸序列为:uucccuuugucauccuaugccu,其序列如seqidno.15所示;
确定丰度所用pcr引物为:
f:tcggttccctttgtcatcct,其序列如seqidno.48所示;
r:gtgcagggtccgaggt,其序列如seqidno.49所示;
针对mir-205,
其核酸序列为:uccuucauuccaccggagucug,其序列如seqidno.16所示;
确定丰度所用pcr引物为:
f:tggtccttcattccaccgg,其序列如seqidno.50所示;
r:gtgcagggtccgaggt,其序列如seqidno.51所示;
针对mir-210,
其核酸序列为:cugugcgugugacagcggcuga,其序列如seqidno.17所示;
确定丰度所用pcr引物为:
f:ggctgtgcgtgtgacagc,其序列如seqidno.52所示;
r:gtgcagggtccgaggt,其序列如seqidno.53所示;
针对mir-301a,
其核酸序列为:cagugcaauaguauugucaaagc,其序列如seqidno.18所示;
确定丰度所用pcr引物为:
f:tcggcagtgcaatagtattgt,其序列如seqidno.54所示;
r:gtgcagggtccgaggt,其序列如seqidno.55所示;以及
针对mir-429,
其核酸序列为:uaauacugucugguaaaaccgu,其序列如seqidno.19所示;
确定丰度所用pcr引物为:
f:gtcggtaatactgtctggtaa,其序列如seqidno.56所示;
r:gtgcagggtccgaggt,其序列如seqidno.57所示。
2.结果
2.1.在iga肾病学中筛选具有改变水平的mirna
igan的确切原因尚未完全了解。microrna可能有助于igan的发病和进展。微rna在血浆中的水平可能反映了血浆中的状态igan,并被用作监测这种疾病的生物标志物。考虑到这一点,本发明首先在未治疗的肾活检已确诊igan患者和健康受试者比较备选microrna水平。使用前述方法,针对前述19micrornas对健康受试者和未治疗的igan患者的表达量的测试结果。发现15个microrna的水平在健康受试者和igan患者之间有显著差异,包括8种microrna的血浆水平显著减少,包括mir-15a,mir-16,mir-21,mir-29a,mir-148b,mir-200c,mir-210和mir-301a;7种microrna的血浆水平显著升高,包括mir-34a,mir-141,mir-155,mir-184,mir-204,mir-205和mir-429(图1)。目前还不清楚,这些micrornas的血浆水平的改变是什么原因或后果肾脏损害的igan。
2.2.血浆微rna的水平对治疗的反应
为了探索这些15种micrornas作为监测igan的生物标志物的潜力,本发明检测了igan治疗后这些microrna的变化情况。本发明收集了19名肾活检证实的igan患者的血浆在开始治疗之前和之后3个月,血清肌酸酐水平和蛋白尿是在治疗后显著下降。并且egfr通过治疗而增加,表明症状得到缓解(表2)。本发明发现14个microrna中有6(mir-29a,mir-141,mir-200a,mir-204,mir-205和mir-429)个在治疗前和治疗后显示不同的表达水平(图2)。除了mir-29a,mir-141,mir-200a,mir-204,mir-205和mir-429全部显示类似的模式(图3),igan诱导的血浆标记物水平变化被治疗逆转,提示这些microrna可能对igan引起的肾脏损害具有保护作用,并预测igan的进展。相比之下,血浆mir-205水平在未治疗的igan患者与健康受试者相比显著升高,经过治疗未能阻止mir-205的增加(图2)。这表明mir-205可能是导致肾脏发病的监控标志物,并且可能是为什么igan不能被目前可用的治疗所促进的机制的基础,突出其作为评估igan状态的生物标志物的价值。通过这种预处理和后处理相比之下,本发明筛选出了无反应的micrornas,并专注于响应micrornas,进行更深入的分析。
2.3.血浆mir-29a,mir-141,mir-200a,mir-204,mir-205和mir-429与蛋白尿,egfr和血清肌酐水平的关联性试验
在鉴定了对igan治疗有反应的6种microrna之后,想知道这些microrna是如何反映igan对肾脏的损害。因此,本发明测试了它们的血浆之间的相关性主要临床参数如igan中的蛋白尿,egfr和血清肌酸酐水平。在收集血浆和尿液时平均接受1年霉酚酸酯(mmf)和强的松松联合治疗的患者(n=79)样本。
治疗方案为:
施用血管紧张素受体阻滞剂(arbs)缬沙坦的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2的病人,每人每日80mg,若出现低血压不能耐受或肌酐进行性升高,减量或停用。
施用霉酚酸酯(mmf)的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2,病理新月体占10-50%的病人。剂量1g至1.5g每天,分两次口服,维持治疗半年后减量,疗程1年半。使用mmf联合强的松,mmf不单用。
施用强的松的步骤为:强的松0.5mg每公斤体重每天,半年后逐步减量,疗程1年半。
联合使用的步骤为:尿蛋白>1g/24小时,egfr>30ml/min/1.73m2,病理新月体占10-50%的病人。施用霉酚酸酯剂量1g至1.5g每天,分两次口服,强的松0.5mg每公斤体重每天,维持治疗半年后减量,疗程1年半。
本发明发现只有mir-29a和mir-205与egfr,蛋白尿和血清肌酸酐水平相关(图4&5),其他microrna与这些临床参数无关(数据未显示)。如预期血浆mir-29a与egfr呈正相关,与蛋白尿和尿蛋白呈负相关血清肌酸酐,证实mir-29a对igan诱导的肾损伤具有保护作用(图4)。与之相反的是,mir-205与egfr呈现相反的相关性,与蛋白尿和尿蛋白呈正相关血清肌酐显示较高的mir-205水平反映了更严重的肾损伤(图5)。值得的注意到这些患者已经接受了治疗并缓解了症状。正如实践中经常看到的一样患者的血清肌酐水平和蛋白尿正常或接近正常,而其他患者仍然高蛋白尿程度和/或高血清肌酐水平。因此,血浆mir-29a和mir-205可以是用于预测个体患者对用霉酚酸酯(mmf)和强的松松联合治疗的反应。在这些患者中,本发明发现了egfr与蛋白尿呈负相关(r=-0.269和p=0.008),与血浆白蛋白呈正相关水平(r=0.237和p=0.023)。这表明在这些患者中egfr,观察蛋白尿和血浆白蛋白水平,验证本发明对关系的观察结果在反映肾功能的临床参数与mir-29a和mir-205之间。
2.4.血浆,但不是尿mir-29a和mir-205预测igan的进展
除了血浆之外,microrna也大量存在于尿液中。本发明想知道是否尿mir-29a、mir-205也可以反映肾脏损害,并可作为生物标志物监测igan的进展。本发明测量了如上所述治疗的igan患者的尿mir-29a和mir-205水平。在尿中检测mir-29a和mir-205,但水平较低(图6),而血浆中mir-29a和mir-205均与尿液中mir-29a和mir-205成正相关,提示尿mir-29a和mir-205可能来源于血液循环。接下来,本发明分析了尿mir-29a和mir-205水平是否与之相关egfr和蛋白尿。出乎意料的是,尿mir-205水平与egfr,蛋白尿或与血清肌酸酐水平无关(图8)。尿mir-29a也与蛋白尿和血清肌酐水平不相关,但与egfr相关(图7)。这表明尿mir-29a和mir-205在预测肾脏损害方面不如其血浆对应物强大。
而mir-29a和mir-205是否可以用来预测iga肾病的进展仍然是一个有趣的问题。然后,本发明分析了在不同阶段igan患者中的血浆mir-29a和mir-205水平使用lee氏分类基于肾活组织检查进行评估。从79名igan患者中,有13名患者在疾病病程阶段2,40名在阶段3,17名在阶段4,9名在阶段5。本发明发现,血浆mir-29a随着igan的进展而减少(图9a)。尿mir-29a显示类似的模式,但是不如血浆mir-29a清晰(图9b)。血浆mir-205水平也预测了igan的进展,类似于mir-29a,而尿mir-205对igan进展没有预测价值(图9c&d)。相关分析证实血浆mir-29a和mir-205a与疾病的严重程度相关相关效率分别为-0.345(p=0.001)和0.218(p=0.029)。综合起来,这些数据提示血浆而非尿mir-29a和mir-205可用于监测肾功能和肾功能igan的进展。
3.讨论
与许多其他研究不同,这些研究仅比较健康受试者中的微rna表达与igan中的微rna表达在这项研究中,本发明用一步一步的方法来筛选可能有潜力microrna生物标志物在监测igan中的价值。首先,本发明筛选了一组microrna。本发明发现了13个microrna与健康受试者相比,这些患者的血浆水平不同。接下来,本发明探讨了这些微rna通过测量其治疗前后的血浆水平来响应治疗耐心。本发明发现只有6个micrornas对治疗有反应,治疗水平。然后,本发明分析了这些microrna与目前用于临床标记物的关系反映接受igan治疗的患者的肾损害。本发明只发现mir-29a和mir-205与血清肌酐水平,egfr和蛋白尿相关,其余与这些相关临床标志物。此外,本发明发现晚期igan阶段的患者(李氏分类)具有接受治疗后更低的mir-29a和更高的mir-205水平。这表明血浆mir-29a和mir-205水平可以用作标记来监测疾病的进展并预测患者治疗后的结果。
本发明发现mir-205水平上调,即使在治疗后也受到调节这表明血浆mir-205水平不受治疗的影响,可能反映永久性肾脏损害。如果确实如此,则mir-205可以用作检测igan并预测的标记患者结果。事实上,本发明发现血浆mir-205水平与egfr,血清肌酐相关性良好水平和蛋白尿,优于肾内mir-205。进一步需要关于mir-205功能的机制研究来阐明其在igan中的作用。
小结
总之,血浆但不是尿mir-29a和mir-205水平反映肾损伤和功能。血浆mir-29a和mir-205水平可用于监测igan的进展。如通过联合mir-29a和mir-205在iga肾病浓度,可准确判断iga肾病发病病程,同时通过治疗后,通过检测mir-29a和mir-205的浓度,如mir-29a显著降低,mir-205显著升高,评估治疗效果。
以上各个实施例只是用于进一步说明本发明,并不是用来限制本发明的保护范围,凡是基于本发明的构思所作出的等同变换及对本发明的各个技术方案显而易见的改进,均落入本发明的保护范围。
序列表
<110>深圳大学
<120>一种用于监测iga肾病的生物标志物
<141>2018-08-15
<160>76
<170>siposequencelisting1.0
<210>1
<211>22
<212>rna
<213>人类(human)
<400>1
uagcagcacauaaugguuugug22
<210>2
<211>22
<212>rna
<213>人类(human)
<400>2
uagcagcacguaaauauuggcg22
<210>3
<211>22
<212>rna
<213>人类(human)
<400>3
uagcuuaucagacugauguuga22
<210>4
<211>22
<212>rna
<213>人类(human)
<400>4
uagcaccaucugaaaucgguua22
<210>5
<211>22
<212>rna
<213>人类(human)
<400>5
uggcagugucuuagcugguugu22
<210>6
<211>22
<212>rna
<213>人类(human)
<400>6
ucccugagacccuaacuuguga22
<210>7
<211>95
<212>rna
<213>人类(human)
<400>7
cggccggcccuggguccaucuuccaguacaguguuggauggucuaauugugaagcuccua60
acacugucugguaaagauggcucccggguggguuc95
<210>8
<211>22
<212>rna
<213>人类(human)
<400>8
ucagugcaucacagaacuuugu22
<210>9
<211>23
<212>rna
<213>人类(human)
<400>9
uuaaugcuaaucgugauaggggu23
<210>10
<211>22
<212>rna
<213>人类(human)
<400>10
uggacggagaacugauaagggu22
<210>11
<211>21
<212>rna
<213>人类(human)
<400>11
cugaccuaugaauugacagcc21
<210>12
<211>22
<212>rna
<213>人类(human)
<400>12
uaacacugucugguaacgaugu22
<210>13
<211>22
<212>rna
<213>人类(human)
<400>13
uaauacugccugguaaugauga22
<210>14
<211>23
<212>rna
<213>人类(human)
<400>14
uaauacugccggguaaugaugga23
<210>15
<211>22
<212>rna
<213>人类(human)
<400>15
uucccuuugucauccuaugccu22
<210>16
<211>22
<212>rna
<213>人类(human)
<400>16
uccuucauuccaccggagucug22
<210>17
<211>22
<212>rna
<213>人类(human)
<400>17
cugugcgugugacagcggcuga22
<210>18
<211>23
<212>rna
<213>人类(human)
<400>18
cagugcaauaguauugucaaagc23
<210>19
<211>22
<212>rna
<213>人类(human)
<400>19
uaauacugucugguaaaaccgu22
<210>21
<211>21
<212>dna
<213>人类(human)
<400>21
ccgggtagcagcacataatgg21
<210>21
<211>16
<212>dna
<213>人类(human)
<400>21
gtgcagggtccgaggt16
<210>22
<211>21
<212>dna
<213>人类(human)
<400>22
ttcggtagcagcacgtaaata21
<210>24
<211>16
<212>dna
<213>人类(human)
<400>24
gtgcagggtccgaggt16
<210>25
<211>21
<212>dna
<213>人类(human)
<400>25
ttcggtagcttatcagactga21
<210>25
<211>16
<212>dna
<213>人类(human)
<400>25
gtgcagggtccgaggt16
<210>26
<211>21
<212>dna
<213>人类(human)
<400>26
ttcggtagcaccatctgaaat21
<210>27
<211>16
<212>dna
<213>人类(human)
<400>27
gtgcagggtccgaggt16
<210>28
<211>19
<212>dna
<213>人类(human)
<400>28
cggtggcagtgtcttagct19
<210>29
<211>16
<212>dna
<213>人类(human)
<400>29
gtgcagggtccgaggt16
<210>30
<211>19
<212>dna
<213>人类(human)
<400>30
tggtccctgagaccctaac19
<210>31
<211>16
<212>dna
<213>人类(human)
<400>31
gtgcagggtccgaggt16
<210>32
<211>21
<212>dna
<213>人类(human)
<400>32
ttcggtaacactgtctggtaa21
<210>34
<211>16
<212>dna
<213>人类(human)
<400>34
gtgcagggtccgaggt16
<210>34
<211>20
<212>dna
<213>人类(human)
<400>34
tcggtcagtgcatcacagaa20
<210>35
<211>16
<212>dna
<213>人类(human)
<400>35
gtgcagggtccgaggt16
<210>37
<211>22
<212>dna
<213>人类(human)
<400>37
ttcggttaatgctaatcgtgat22
<210>37
<211>16
<212>dna
<213>人类(human)
<400>37
gtgcagggtccgaggt16
<210>38
<211>19
<212>dna
<213>人类(human)
<400>38
cggtggacggagaactgat19
<210>39
<211>16
<212>dna
<213>人类(human)
<400>39
gtgcagggtccgaggt16
<210>40
<211>20
<212>dna
<213>人类(human)
<400>40
gtcggctgacctatgaattg20
<210>41
<211>16
<212>dna
<213>人类(human)
<400>41
gtgcagggtccgaggt16
<210>42
<211>21
<212>dna
<213>人类(human)
<400>42
ttcggtaacactgtctggtaa21
<210>43
<211>16
<212>dna
<213>人类(human)
<400>43
gtgcagggtccgaggt16
<210>45
<211>21
<212>dna
<213>人类(human)
<400>45
ttcggtaatactgcctggtaa21
<210>45
<211>16
<212>dna
<213>人类(human)
<400>45
gtgcagggtccgaggt16
<210>46
<211>20
<212>dna
<213>人类(human)
<400>46
cggtaatactgccgggtaat20
<210>47
<211>16
<212>dna
<213>人类(human)
<400>47
gtgcagggtccgaggt16
<210>48
<211>20
<212>dna
<213>人类(human)
<400>48
tcggttccctttgtcatcct20
<210>49
<211>16
<212>dna
<213>人类(human)
<400>49
gtgcagggtccgaggt16
<210>50
<211>19
<212>dna
<213>人类(human)
<400>50
tggtccttcattccaccgg19
<210>51
<211>16
<212>dna
<213>人类(human)
<400>51
gtgcagggtccgaggt16
<210>52
<211>18
<212>dna
<213>人类(human)
<400>52
ggctgtgcgtgtgacagc18
<210>53
<211>16
<212>dna
<213>人类(human)
<400>53
gtgcagggtccgaggt16
<210>54
<211>21
<212>dna
<213>人类(human)
<400>54
tcggcagtgcaatagtattgt21
<210>55
<211>16
<212>dna
<213>人类(human)
<400>55
gtgcagggtccgaggt16
<210>56
<211>21
<212>dna
<213>人类(human)
<400>56
gtcggtaatactgtctggtaa21
<210>57
<211>16
<212>dna
<213>人类(human)
<400>57
gtgcagggtccgaggt16
<210>58
<211>50
<212>dna
<213>人类(human)
<400>58
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcacaaa50
<210>59
<211>50
<212>dna
<213>人类(human)
<400>59
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcgccaa50
<210>60
<211>50
<212>dna
<213>人类(human)
<400>60
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcaacat50
<210>62
<211>50
<212>dna
<213>人类(human)
<400>62
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaaccga50
<210>62
<211>50
<212>dna
<213>人类(human)
<400>62
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacaacc50
<210>64
<211>50
<212>dna
<213>人类(human)
<400>64
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcacaag50
<210>65
<211>50
<212>dna
<213>人类(human)
<400>65
gtgcagggtccgaggtcagagccacctgggcaatttttttttttccatct50
<210>65
<211>50
<212>dna
<213>人类(human)
<400>65
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacaaag50
<210>66
<211>50
<212>dna
<213>人类(human)
<400>66
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacccct50
<210>67
<211>50
<212>dna
<213>人类(human)
<400>67
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaccctt50
<210>68
<211>50
<212>dna
<213>人类(human)
<400>68
gtgcagggtccgaggtcagagccacctgggcaatttttttttttggctgt50
<210>69
<211>50
<212>dna
<213>人类(human)
<400>69
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacatcg50
<210>70
<211>50
<212>dna
<213>人类(human)
<400>70
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcatcat50
<210>71
<211>50
<212>dna
<213>人类(human)
<400>71
gtgcagggtccgaggtcagagccacctgggcaatttttttttttccatca50
<210>72
<211>50
<212>dna
<213>人类(human)
<400>72
gtgcagggtccgaggtcagagccacctgggcaatttttttttttaggcat50
<210>73
<211>50
<212>dna
<213>人类(human)
<400>73
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcagact50
<210>74
<211>50
<212>dna
<213>人类(human)
<400>74
gtgcagggtccgaggtcagagccacctgggcaatttttttttttcagccg50
<210>75
<211>50
<212>dna
<213>人类(human)
<400>75
gtgcagggtccgaggtcagagccacctgggcaatttttttttttgctttg50
<210>76
<211>50
<212>dna
<213>人类(human)
<400>76
gtgcagggtccgaggtcagagccacctgggcaatttttttttttacggtt50
- 还没有人留言评论。精彩留言会获得点赞!