一种斑马鱼心脏特异表达模型的构建方法及相关载体与流程
本发明涉及基因工程领域,具体涉及一种斑马鱼心脏特异表达模型的构建方法及相关载体。
背景技术
斑马鱼是目前应用广泛的一种模式动物,在发育生物学领域具有举足轻重的地位。斑马鱼在胚胎发育研究中,有很多优越性,其胚胎发育快,器官发育进程明显,易于追踪检测。目前已经用于的心脏模型、脑模型、肝脏模型、眼模型等的构建,是热门的动物模型,特别是在发育生物学领域。随着双光子干涉显微镜的应用,在体实时观察成为有效的手段。
在分子生物学研究中,用crispr/cas9技术产生dna的双链缺失,提供了新的基因敲除、基因敲入和各种基因组重排,如染色体缺失、反转、重复和易位的途径。目前,迅速发展的微同源末端接合mmej机制,已经发现可以替代传统的双链缺失修复途径,稳定地用于工具酶介导的基因敲除实验。进一步的研究表明nhej,hr和mmej在不同的细胞核动物模型中双链缺失修复效率是不同的,mmej在哺乳动物细胞和模式动物,如斑马鱼小鼠、大鼠、等,表现得更加高效。cre/loxp技术,包括cre重组酶由大肠杆菌噬菌体p1的cre基因编码,是由343个氨基酸组成的38kd的蛋白质,它不仅具有催化活性,而且与限制酶相似,能够特异性识别loxp位点;loxp位点长为34bp,包括两个13bp的反向重复序列和一个8bp的间隔区域。其中,反向重复序列是cre重组酶的特异识别位点,而间隔区域决定了loxp位点的方向。
目前尚未有斑马鱼心脏模型构建的报道。
技术实现要素:
本发明的目的是提供一种斑马鱼心脏特异表达模型的构建方法及相关载体,该方法是一种crispr/cas9介导的、在斑马鱼色素基因内整合心脏特异表达的启动子,启动下游荧光报告基因等的表达可以通过显微镜捕捉荧光信号,同时通过色素衰退辅助筛选,构建成斑马鱼心脏特异表达模型,待斑马鱼成年后,通过对下一代斑马鱼受精卵注射cre酶,可以特异性将loxp位点之间引入的外源序列删除,恢复色素基因表达,达到对插入片段的调控表达。其主要原理是:首先应用crispr/cas9技术,在斑马鱼色素基因内靶向剪切形成双链断裂,结合mmej机理提高微同源重组的效率,将外源片段引入;其次,构建的同源重组载体是针对色素基因设计的,敲除色素基因后可以影响色素合成导致斑马鱼黑色素合成障碍,不但可以作为辅助筛选标记,而且利于心脏的观察;再次,利用mmej机理将靶点两侧上下游各40bp作为同源序列,同时加入egfp报告基因或者需要在心脏特异表达的目的基因,通过获得egfp表达的阳性斑马鱼个体,从而构建成可以通过荧光实时检测的斑马鱼心脏特异表达模型;最后,利用cre/loxp技术,待斑马鱼成年后,通过对下一代斑马鱼受精卵注射cre酶mrna或者表达cre的斑马鱼品系进行交配,可以特异性将同向排列的loxp位点之间引入的外源序列删除,恢复色素基因表达,达到对插入片段的调控表达。依靠以上优势,可以快速构建斑马鱼心脏特异表达模型,同时可以调控插入基因的表达。
为了实现上述目的,本发明的技术方案如下:
一种插入片段,包括斑马鱼心脏特异表达的启动子、融合loxp位点序列的左侧同源臂和右侧同源臂、内部核糖体进入位点、报告基因、转录终止信号片段;其中,所述启动子位于报告基因上游,所述终止信号位于报告基因下游,左侧同源臂位于启动子上游,右侧同源臂位于终止信号下游,同源臂的内侧(即3’端)含有loxp序列;左侧同源臂和右侧同源臂靶向斑马鱼色素基因。
插入片段还可以包括位于所述启动子和报告基因之间的多克隆位点,多克隆位点可以用于插入外源目的基因,研究该外源目的基因对心脏发育的影响研究。
插入片段也即同源重组基因片段,具体的,所述的左侧同源臂和右侧同源臂之间依次设有以下所述的元件:斑马鱼心脏特异表达的启动子、多克隆位点、内部核糖体进入位点、报告基因和转录终止信号片段。
所述启动子为ztnnt2-promoter,其核苷酸序列为如seqidno.21所示。
可选地,cre/loxp位点或称loxp位点,本发明中使用的同链同向时删除插入片段的调控模式,如研究人员有需要可以使用其他三种特性,进行表达的调控,分别是:两个loxp位点共链反向时,cre重组酶诱导loxp间的序列翻转;两个loxp位点异链或异染色体时,cre重组酶诱导两条dna链发生交换或染色体易位;当四个loxp位点分别位于异链或异染色体上,cre重组酶诱导loxp间的序列互换。cre酶编码区的序列如seqidno.27所示。
可选地,所述的报告优选荧光报告基因;如egfp基因(enhancedgreenfluorescentprotein)(seqidno.22)、gfp、rfp、yfp、mcherry等任意荧光蛋白基因;可选地,所述的转录终止信号为sv40polya(simianvacuolatingvirus40polya)、其核苷酸序列为seqidno.24,其他的终止信号也可以如β-globinteminator或者bghpolya(bovinegrowthhormonepolya),其核苷酸序列分别为seqidno.25和seqidno.26。内部核糖体进入位点(internalribosomeentrysite,ires)的序列如seqidno.28。
优选地,左侧同源臂和右侧同源臂使用的是mmej方式进行微同源重组,效率更高,靶向斑马鱼色素基因,包括但不限于使用tyrosinase基因(daniorerio,geneid:30207)作为靶向基因,其优点如下:1)它是目前斑马鱼已知的编码酪氨酸酶的基因;2)它的作用主要体现在影响黑色素生成,研究表明该表型不会影响胚胎个体的发育;3)作为靶标基因,突变后在斑马鱼胚胎发育早期24hpf-120hpf,有着及其明显的白化表型,易于进行斑马鱼心脏的在体观察。
本发明还提供了含有所述插入片段的同源重组载体、细胞或工程菌。重组载体包括原始载体及插入原始载体的上述插入片段;其中,原始载体可以但不限于t载体。
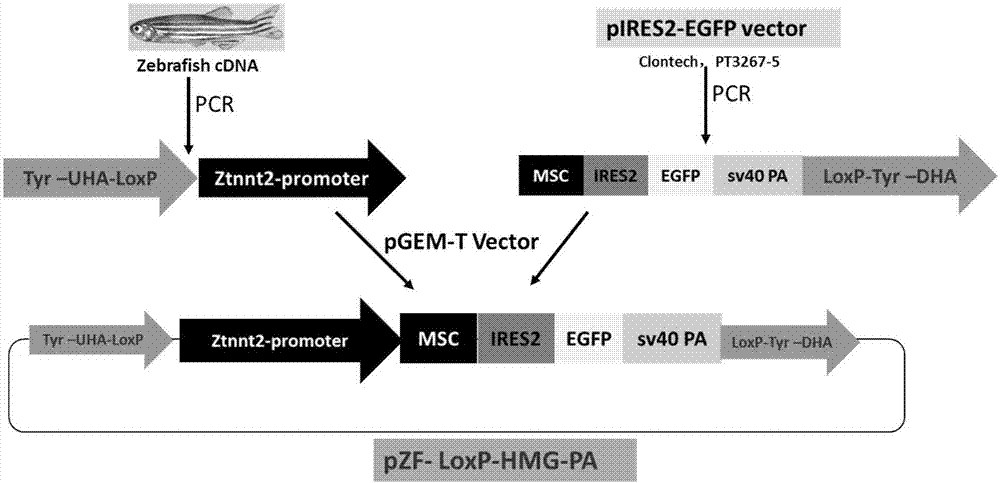
一种同源重组载体的构建方法如下:以斑马鱼cdna为模板,以ztnnt2-f和ztnnt2-r为引物进行扩增后,再以该扩增产物为模板,以lz-f和lz-r为引物进行第二轮扩增,得片段1;用特异性引物从pires2-egfp(clontech,pt3267-5)载体上扩增ires-egfp-pa,与上述片段1进行连接,然后连入用ncoi和spei酶切的pgem-teasyvector中。
本发明还公开了一种斑马鱼心脏特异表达模型的构建方法,包括:
1)构建所述的同源重组载体,获得所述插入片段;
2)设计针对同源臂靶向基因的特异性靶点,合成相应的sgrna,合成cas9-mrna;
3)将所获得sgrna、cas9-mrna和插入片段转入斑马鱼受精卵中,筛选转基因斑马鱼。
步骤3)中,在斑马鱼发育至24hpf(hourspostfertilization)早期心脏搏动开始,即可以筛选获得心脏表达egfp基因的阳性个体,24hpf后由于色素基因被阻断表达,阳性个体无色素沉积,利于心脏在体观察检测。在斑马鱼成年后,筛选实验需求的特定心脏表型,通过cre酶可以特异性将loxp位点之间引入的外源序列删除,恢复色素基因的表达,达到调控插入基因表达的目的,恢复无外源基因插入的斑马鱼群体。
本发明结合crispr/cas9、mmej和cre/loxp三种技术,获得一种斑马鱼心脏特异表达模型构建和调控表达的方法,为心脏模型的构建和调控研究,提供了高效的方法。使用荧光表达基因作为标签,可以有效的实时显示心脏的表达模式。同时,在多克隆位点插入其他功能基因时,可以作为研究该基因对心脏发育的影响研究,通过标签基因显示心脏变化,同时可以通过cre/loxp技术恢复表型。研究中使用络氨酸酶基因作为整合的靶点,插入色素基因,可以导致斑马鱼黑色素合成障碍,产生白化表型。在原基-5期(24hpf)之后,斑马鱼心脏的跳动产生,同时黑色素细胞也开始成串排列,形成黑色素斑块,影响心脏的在体观察。通常的做法是用ptu处理使斑马鱼透明,但其对斑马鱼早期神经细胞产生有抑制作用,影响斑马鱼早期神经发育。但是,敲除色素基因对斑马鱼发育没有显著影响,同时斑马鱼发育的研究过程中涉及到在体实时观察检测,选择色素基因利于后期观察。通过本发明的方法,不但可以快速建立在斑马鱼心脏特异表达基因的转基因模型,同时可以根据实验需求及时调控插入片段的表达。
具体的,本发明的技术方案达到的有益效果是:
1)本方法使用crispr/cas9系统介导,将目的基因序列靶向导入色素基因中,通过斑马鱼心脏表达egfp基因的表达进行筛选。与现有应用于斑马鱼上的转基因方法相比,如转座子、慢病毒载体等比较,本发明提供方法靶向精确、生物安全性高、不会引入未知突变。同时基因表达效果明显,而且不会引入影响胚胎发育的因素。同时,由于色素的退化,斑马鱼得早期胚胎检测,更容易通过显微镜进行活体跟踪监测。
2)本发明使用的cre/loxp技术,通过将loxp位点插入宿主基因组内,注射cre重组酶或者与表达cre的斑马鱼系交配,与loxp位点两端的反向重复序列区形成二聚体,进一步其他loxp位点的二聚体结合形成四聚体,cre重组酶切下loxp位点之间的dna,再通过dna连接酶重新连接。loxp位点的位置和方向决定了重组的结果。本研究中采用两个loxp位点共链同向时,cre重组酶敲除loxp间的序列的方式调控基因的表达。由于cre酶的高效性、重组过程的简单性、loxp序列的唯一性,以及cre重组酶可以在生物体不同组织和不同生理条件下发挥作用,,使用该系统可以高效的进行调控,现有技术中未涉及cre/loxp技术用于精确位点删除以及与其他两种技术结合的报道;且研究发现,本发明添加loxp位点后并不影响色素基因的敲除效率及外源目的基因的表达。
3)本方法所使用的ncas9(addgene,plasmid#46757)是针对物种斑马鱼进行过密码子优化过的cas9表达载体,从而提高了靶向切割效率,再经过高效的体外转录试剂盒(life,am1348),体外转录合成ncas9-mrna,与sgrna体外转录产物和同源重组dna片段,三者共注射斑马鱼受精卵,以mrna的形式注射替代cas9载体dna片段注射,符合了斑马鱼胚胎发育快的特性,满足了斑马鱼显微注射的要求。
4)通过crispr/cas9系统靶向基因组dna序列的特异性,mmej的同源重组方式也进一步提高了整合片段的特异性和方向性,因此本发明所述的方法能够高效地将同源重组片段靶向插入宿主靶基因。本发明在报告基因上游预留了一个mcs位点,可插入功能基因。同时,由于报告基因和待插入mcs位点的基因共用一个相同的心脏特异性启动子,并且有ires的存在,能够保证两个基因在基因组中共转录,但不会共翻译形成融合蛋白。
5)本发明所用的心脏启动子为心肌肌钙蛋白t的强启动子,选择该启动子是由于该启动子是研究肌原纤维形成和基于肌节的心脏病的有价值的体内模型,与其他启动子比较在构建模型上更有优势,特别是研究发育和肌节心脏病模型上。
6)本发明所述的方法,适用于斑马鱼心脏功能的研究、模型的构建,及表达的调控。本发明提供包含表达目的基因和egfp基因的同源重组载体,专业人员可以参考本方法的敲除位点和同源臂;也可以在tyrosinase基因设计其他靶点,同时设计新的同源臂;或者在其他色素基因如kit、gol等,设计新的靶点。
附图说明
图1为同源重组载体pzf-loxp-hmg-pa构建过程示意图;图中分别pcr扩增启动子和报告基因片段,二者连接后,插入pgem-tvector,获得同源重组载体pzf-loxp-hmg-pa;
图2为ztnnt2-promoter斑马鱼心脏特异表达启动子扩增电泳图;在启动子上游添加40bp的同源臂lhr和酶切位点ncoi,以及34bp长的loxp位点,最终大小为1166bp,m表示dl2000marker。
图3为ires-egfp-pa-loxp片段扩增电泳图;在polya下游添加40bp的同源臂、酶切位点和loxp位点,最终大小为1675bp,m表示dl2000marker。
图4为靶向色素基因的同源重组作用机制简图;设计的靶点针对tyr-cds1区,在靶点的上下游分别设计40bp长度的mmej微同源臂,通过同源重组方式整合到基因组中;
图5为ncas9转录结果图;其中m代表rnahrmarker,1代表ncas9-mrna纯化产物,2代表ncas9体外转录线性化的模板,
图6为同源重组载体uha-he-dha插入斑马鱼后gfp表达图;图6(1)是硬骨鱼类心脏模式图;图6(2)是转基因检测图:对比明场图a和b,可以很明显的看到色素消退;荧光图片c1,是在40倍下检测,可以看到在心脏的特异表达,c2是在100倍下的检测,更加清晰看到表达绿色荧光的房室结构。
图7为同源重组基因片段uha-he-dha表达插入验证图;图中表示引物设计扩增的模式图。
图8为同源重组基因片段uha-he-dha表达插入验证图。图中表示uha-he-dha插入验证的电泳图,内参ef1a表明斑马鱼dna可用于检测,m表示dl2000marker。
图9为cre/loxp调节作用图;图中a、c为转基因鱼f1代3月龄筛选图,a为母鱼,c为公鱼;b为筛选的后代,1月龄图;d图为纯合的转基因鱼与转cre鱼后代,删除了位点恢复表型的鱼,3月龄图;e为b剪尾鉴定后的测序比对图,表明了插入,下划线为loxp位点的序列。
图10为trdmt1基因扩增结果图。图中为trdmt1基因的cdsq区,m表示dl2000marker。
图11为trdmt1基因插入检测结果图。图中检测产物引物上游位于载体,下游引物位于插入片段,扩增长度748bp,m表示dl2000marker。
具体实施方式
为了阐明本发明的技术方案及技术目的,下面结合附图及具体实施方式对本发明做进一步的介绍。下述实施例中的方法,如无特别说明,均为常规方法。
实施例1
本实施例1提供了通过心脏特异性启动子在心脏表达egfp基因的方案。构建含有egfp报告基因的转基因同源重组载体pzf-loxp-hmg-pa载体,利用crispr/cas9介导的双链缺口,将其通过mmej方法插入tyrosinase基因第一个外显子区域,在终止tyrosinase基因的表达同时插入报告基因,最后通过报告基因和色素基因双重筛选,获得心脏表达目标基因的斑马鱼个体。
本实施例1具体包括以下步骤:
1.构建含有包含报告基因的同源重组载体pzf-loxp-hmg-pa,并且获得可以用于斑马鱼注射的片段。
1.1靶向性位点和同源重组的上下游同源臂的设计。
本研究室已经通过筛选获得,高效的针对tyrosinase基因的靶点,该筛选过的靶点为tyrosinase-sgrna1。以这个靶点为基础,设计上游和下游设计微同源臂tyrosinase-sg1-uha和tyrosinase-sg1-dha,靶点tyrosinase-sgrna1下用下划线表示,其核苷酸序列如下:
tyrosinase-sgrna1:5’-ggactggaggacttctgggg-3’(seqidno.1);
tyrosinase-sg1-uha:
5’-agctcgtctctccagcagttcccccgagtctgcacctccc-3’(seqidno.2);
tyrosinase-sg1-dha:
5’-ggccagactggacagcagcgtttggactggaggacttctg-3’(seqidno.3);
1.2扩增ztnnt2-promoter启动子。
以斑马鱼cdna为模板,使用高保真酶(phantahssuper-fidelitydnapolymerase,vazyme)扩增1058bp(seqidno.21)的ztnnt2-promoter基因。进行两轮pcr,第一轮设计扩增引物为:ztnnt2-f和ztnnt2-r,其中ztnnt2-f的上游加上34bp的loxp位点(seqidno.23)。在下游引物上添加多酶切位点xhoi-bglii-afei-bmti-nhei,扩增产物为1126bp。第二轮,再以第一轮扩增产物为模版,以lz-f和lz-r为引物,其中lz-f上游包括酶切位点ncoi和一个40bp长的tyrosinase-sg1-uha,扩增获得1166bp结果,扩增结果如附图2所示。
50μl反应体系包括:第一轮100ng的斑马鱼cdna作为模板,第二轮以第一轮产物为模板,1μl(10μm)上下游引物,1μldnapolymerase,10μl5xsfbuffer,1μl(10μm)dntpmix和32μlddh2o。其反应条件为:95℃5min;95℃10s,(第一轮56℃30s、第二轮58℃30s)72℃1min30s,35x循环;72℃10min,4℃维持。
所用引物ztnnt2-f和ztnnt2-r的核苷酸和酶切位点序列(大写字母)如下,其中lz-f的上游添加的同源臂小写,酶切位点斜体大写,loxp位点和多酶切位点大写有下划线标记;ztnnt2-f上游包括一个34bp长的loxp位点有下划线,ztnnt2-r的酶切位点大写,具体如下:
ztnnt2-f:5’-ataacttcgtatagcatacattatacgaagttatctctgatgaatttgctgtg-3’(seqidno.4)
ztnnt2-r:5’-ctcgagatctgagtccggtagcgctagctgacacgcagcagagatgcagag-3’(seqidno.5)
lz-f:5’-ccatggagctcgtctctccagcagttcccccgagtctgcacctcccataacttcgtatagcataca-3’(seqidno.6)
lz-r:5’-ctcgagatctgagtccggtagcgctagctgac(seqidno.7)
1.3转基因表达载体pzf-loxp-hmg-pa的构建。
用特异性引物从pires2-egfp(clontech,pt3267-5)载体上扩增ires-egfp-pa,1675bp,然后与上述ztnnt2-promoter片段进行连接,16℃连接16h。用ncoi和spei酶切pgem-teasyvector,将上述连接产物插入,形成表达载体框架pzf-loxp-heart-mcs-egfp-pa,命名pzf-loxp-hmg-pa。此外,载体包含多克隆位点,若插入目的基因序列,即可形成在心脏特异性表达特定基因的转基因同源重组载体。
进行两轮扩增,第一轮设计扩增引物为:igp-f和igp-r,其中igp-f添加xhoi位点,lpa-r添加40bp的同源臂tyrosinase-sg1-rhr,同时在酶切位点上游添加t,扩增产物大小为1640bp;第二轮设计引物,igp-f和lpa-r,其中lpa-r包括酶切位点spei,和34bp长的loxp位点,扩增产物1675bp,扩增结果如附图3所示。
50μl反应体系包括:第一轮以10ng的pires2-egfp质粒作为模板,第二轮以第一轮产物为模版,1μl(10μm)上下游引物,1μldnapolymerase,10μl5xsfbuffer,1μl(10μm)dntpmix和32μlddh2o。其反应条件为:95℃5min;95℃10s,(第一轮62℃30s;第二轮,60℃30s),72℃2min,35x循环;72℃10min,4℃维持。
所用引物igp-f和igp-r的核苷酸序列(大写字母)如下,其中igp-f上游添加xhoi位点(小写字母),t为大写,igp-r添加loxp位点有下划线,lpa-r添加酶切位点spei(大写字母)和40bp同源臂(小写字母);。
igp-f:5’-tctcgagaattctgcagtcgacggtac-3’;(seqidno.8)
igp-r:5’-ataacttcgtatagcatacattatacgaagttattaagatacattgatgagttt-3’;(seqidno.9)
lpa-r:5’-actagtggccagactggacagcagcgtttggactggaggacttctgataacttcgtatagcataca-3’;(seqidno.10)
1.4用于注射的转基因载体的线性化片段的获取。
最终形成的pzf-loxp-hmg-pa载体需要进行pcr扩增,获得用于注射的uha-he-dha,设计引物he-f和he-r用于扩增,核苷酸序列如下:
he-f:5’-agctcgtctctccagcagtt-3’;(seqidno.11)
he-r:5’-cgctgctgtccagtctggcc-3’;(seqidno.12)
100μl反应体系包括:200ng的pzf-loxp-hmg-pa作为模板,2μl(10μm)he-f引物,2μl(10μm)he-r引物,2.5μldnapolymerase,20μl5xsfbuffer,2μl(10μm)dntpmix和ddh2o补齐至100μl。其反应条件为:95℃5min;95℃10s,60℃30s,72℃5min,30x循环;72℃10min;4℃维持。
将扩增后的片段通过1%的琼脂糖凝胶检测大小,电泳检测目标片段。用纯化试剂盒纯化该片段,用无酶水溶解,nanodrop测定浓度后,用于注射,同源载体片段整合到基因组中的原理如图4。
2.同源重组基因片段uha-he-dha、tyrosinase-sgrna1和cas9-mrna共注射与筛选。
2.1注射所用ncas9-mrna的合成与制备。
用xbai酶切质粒ncas9载体(addgene,plasmid#46757),获得7300bp左右的线性化片段,用酚氯仿抽提纯化后作为转录模板。通过体外转录试剂盒进行转录,转录产物使用酚氯仿抽提纯化,获得用于斑马鱼注射的4200bp左右的ncas9-mrna(结果如图5)。
体外转录20μl反应体系:10μlt32xntp/cap,2μlt3enzymemix,2μl10xt3reactionbuffer,0.1–1μg线性化templatedna,(1μl)(optional)[α-32p]utpasatracer,nuclease-freewater补齐到20μl。反应条件:置于pcr仪,37℃,恒温反应4h;加入1μldnase处理15min,去除转录模版,将转录产物进行纯化处理,获得用于注射ncas9-mrna。tyrosinase-sgrna1由本研究所合成保存。
2.2斑马鱼的显微注射。
显微注射液置于冰上混合:包括uha-he-dha、tyrosinase-sgrna1和cas9-mrna(注射三者的浓度质量分数比例为3:1:2),以及酚红和无酶水。斑马鱼由中国科学院水生生物研究所(中国,武汉)提供ab系种鱼。将斑马鱼以公:母=1:2的比例进行配对,置于繁殖盒中,执行光周期(14小时日光和10小时黑暗)。第二天换水后,拔开隔板,待交配后,计时15min收卵,除去死卵。待斑马鱼受精卵动物极呈现突口状,在显微注射仪下进行受精卵显微注射。注射完毕后,将斑马鱼卵转移至斑马鱼胚胎孵化培养液,置于28.5℃培养。
2.3注射后斑马鱼心脏表达基因的筛选。
注射后斑马鱼胚胎培养至24hpf,发育时间点为原基-5期,这个阶段斑马鱼黑色素细胞开始聚集成团,在高倍镜下可以见到色素团。同时,斑马鱼心脏在这个时期出现了早期心脏的搏动。在荧光显微镜下直接可以观测到心脏有荧光表达。通过6次独立试验,在3dpf检测荧光表达效率,结果为37.35±1.4%(mean±sem)。同时,在白光下还可以直观地通过体色是否白化来进行筛选,只要是基因敲除的鱼就会有白化的发生,剔除没有发生白化的个体。再进一步通过荧光标签筛选转基因鱼。
转基因载体插入斑马鱼后gfp表达图6。图6(1)是硬骨鱼类心脏模式图,包括静脉窦,一心房和一心室等。图6(2)是转基因检测图:对比明场图a和b,可以明显地看到色素消退;荧光图片c1,是在40倍放大下检测到插入gfp表达,可以看到在心脏的特异性表达,c2是在100倍放大条件下的图片,更加清晰地看到表达绿色荧光的房室结构。
2.4注射后基因组整合的检测。
为了进一步验证lhr-he-rhr整合到斑马鱼的基因组上,设计针对插入位点的引物,扩增接口处目的片段。扩增模式如图7,pcr结果如图8所示,可见该位点有同源重组的片段的插入,成功获得心脏特异表达基因的斑马鱼。
验证引物分别为he-test-f和he-test-r,内参引物分别为ef1a-f/r,核苷酸序列如下:
he-test-f:5’-gcgtctcactctcctcgact-3’;(seqidno.13)
he-test-r:5’-catgtcaggtgtcctgacata-3’;(seqidno.14)
ef1a-f:5’-cattaacatcgtggttattggcc-3’;(seqidno.15)
ef1a-r:5’-atcaactatagtcaagttagacc-3’;(seqidno.16)
2.5cre/loxp调控插入片段的表达
斑马鱼使用cre酶有两种方式,受精卵注射注射cre重组酶mrna(编码序列如seqidno.27)或者与表达cre的斑马鱼系交配。由于本研究室育有可以表达cre的斑马鱼品系,故此处采用交配筛选的方式进行cre/loxp调控。将筛选的斑马鱼心脏模型培养至成年,进行群内交配,筛选双等位基因插入的雌雄个体,进行纯合筛选,获得纯合表达斑马鱼。再与cre的斑马鱼品系交配,发现白化表型消除,随后扩增插入片段发现插入片段的缺失。
实施例2
本实施例为了证实在本研究所构架的载体pzf-loxp-hmg-pa的msc位点可以插入克隆基因,选择的基因为斑马鱼trdmt1基因(ncbi:nm_001018143.1),将克隆的cds序列插入载体的多克隆位点,通过pcr鉴定插入。
(1)将载体扩增酶切后备用
将载体菌种接种至lb液体培养基中,过夜37℃培养,用omega质粒提取试剂盒提取质粒,用bglii进行酶切后,备用。酶切方式如下示例所示。
5'-a↓gatct-3'
3'-tctag↑a-5'
(2)获得插入trdmt1片段的cds序列
从斑马鱼cdna中扩增出1146bp的trdmt1基因的cds序列,扩增引物为tr-f和tr-r,并在引物5’端添加酶切位点,扩增结果见图10,引物序列如下,扩增的斑马鱼trdmt1基因cds区序列大小为1146bp。
50μl反应体系包括:100ng的斑马鱼cdna作为模板,1μl(10μm)上下游引物,1μldnapolymerase,10μl5xsfbuffer,1μl(10μm)dntpmix和32μlddh2o。其反应条件为:95℃5min;95℃10s,58℃30s,72℃1min30s,35x循环;72℃10min,4℃维持。
tr-f:5’-gatcatggagaacacggagcgact-3’;(seqidno.17)
tr-r:5’-gatcctattttgagagcattagac-3’;(seqidno.18)
(3)将基因插入载体
将获得的片段插入载体,连接酶体系为:插入片段和载体摩尔比为:5:2。反应条件:16℃,16h。获得连接产物,转化后涂板,提取载体质粒。并且设计引物扩增验证,扩增结果如图11,设计引物trt-f和trt-r,扩增产物748bp,引物如下所示。
50μl的pcr反应体系包括:10ng载体质粒,1μl(10μm)上下游引物,1μldnapolymerase,10μl5xsfbuffer,1μl(10μm)dntpmix和32μlddh2o。其反应条件为:95℃5min;95℃10s,59℃30s,72℃1min,35x循环;72℃10min,4℃维持。
trt-f:5’-atttaggtgacactatagaa-3’;(seqidno.19)
trt-r:5’-tctaggctcagatacttcct-3’;(seqidno.20)
(4)利用步骤(3)获得的转基因载体,克隆出同源重组基因片段后与tyrosinase-sgrna1和cas9-mrna转入斑马鱼中,筛选获得转基因斑马鱼。
经验证,外源目的基因成功转入斑马鱼内,并表达。将转基因斑马鱼培养至成年,将筛选的斑马鱼心脏模型培养至成年,进行群内交配,筛选双等位基因插入的雌雄个体,进行纯合筛选,获得纯合表达斑马鱼。再与cre的斑马鱼品系交配,发现白化表型表型消除,随后扩增插入片段发现插入片段的缺失。
以上显示和描述了本发明的基本原理、主要特征和本发明的优点。本行业的技术人员应该了解。本发明不受上述实施例的限制,上述实施例和说明书中描述的只是说明本发明的原理,在不脱离本发明精神和范围的前提下,本发明还会有各种变化和改进,本发明要求保护范围由所附的权利要求书、说明书及其等效物界定。
序列表
<110>扬州大学
<120>一种斑马鱼心脏特异表达模型的构建方法及相关载体
<160>28
<170>siposequencelisting1.0
<210>1
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>1
ggactggaggacttctgggg20
<210>2
<211>40
<212>dna
<213>人工序列(artificialsequence)
<400>2
agctcgtctctccagcagttcccccgagtctgcacctccc40
<210>3
<211>40
<212>dna
<213>人工序列(artificialsequence)
<400>3
ggccagactggacagcagcgtttggactggaggacttctg40
<210>4
<211>53
<212>dna
<213>人工序列(artificialsequence)
<400>4
ataacttcgtatagcatacattatacgaagttatctctgatgaatttgctgtg53
<210>5
<211>51
<212>dna
<213>人工序列(artificialsequence)
<400>5
ctcgagatctgagtccggtagcgctagctgacacgcagcagagatgcagag51
<210>6
<211>66
<212>dna
<213>人工序列(artificialsequence)
<400>6
ccatggagctcgtctctccagcagttcccccgagtctgcacctcccataacttcgtatag60
cataca66
<210>7
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>7
ctcgagatctgagtccggtagcgctagctgac32
<210>8
<211>27
<212>dna
<213>人工序列(artificialsequence)
<400>8
tctcgagaattctgcagtcgacggtac27
<210>9
<211>54
<212>dna
<213>人工序列(artificialsequence)
<400>9
ataacttcgtatagcatacattatacgaagttattaagatacattgatgagttt54
<210>10
<211>76
<212>dna
<213>人工序列(artificialsequence)
<400>10
actagtggccagactggacagcagcgtttggactggaggacttctgataaactagtataa60
cttcgtatagcataca76
<210>11
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>11
agctcgtctctccagcagtt20
<210>12
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>12
cgctgctgtccagtctggcc20
<210>13
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>13
gcgtctcactctcctcgact20
<210>14
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>14
catgtcaggtgtcctgacata21
<210>15
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>15
cattaacatcgtggttattggcc23
<210>16
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>16
atcaactatagtcaagttagacc23
<210>17
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>17
gatcatggagaacacggagcgact24
<210>18
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>18
gatcctattttgagagcattagac24
<210>19
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>19
atttaggtgacactatagaa20
<210>20
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>20
tctaggctcagatacttcct20
<210>21
<211>1058
<212>dna
<213>斑马鱼(barchydanioreriovar)
<400>21
ctctgatgaatttgctgtgtatgtagttgaagtcagaattattagccctcttcgattttt60
ttttcttcttttttaaatattttccaaatgatgatttacagagcaaggaaattttcacag120
tatgtctgataatatttttttattctggagaaagacttatttgttttatttcggctagaa180
ttaatagttattaattttttaaacacaattttagggacaaaattttttagcccctttaag240
ttatactcgatagttcacagaacaaaccattgttatacaataacttgctgaattatccta300
acctaattaccctagttaatcctttaaatgtcactttaagctgtatagaagtgtcttgaa360
aaatatctagttaaatattatgtactgtcatcatggcaaagataaagtaaatgagttagt420
agaaatgacttattaaaactattatgttcagaaatgtcttgaaaaaatcttctctccgtt480
aaacagaaattgggtaaaaaataaacaagcagtctaataattcaggggagctaataattc540
aaacttcagctgtatgtcaggacacctgacatgccagtacagtgggtggggagaactcat600
ttgcatttaaaggcacaggcacaatacagctaaaattccctctaaccccaaatggatttt660
tgagctgaaacatcaaccacagattttggagacaccaaagacttaatttaaatcatgtaa720
ataggggcatagaagcccttacaacatcctctgggacatgtgaaggccttcagtgccagt780
ctggtggcgtgagcaaacatgaagaaagcgctgagagattaaccagtgcacgtgttatca840
gacgacagcagaatagacctgtgttgatatctgtgtttatctccatactcctcactataa900
caattgctgcagccttttagggagcaggactgttctccacttatcagtgagggtaaaaat960
aaacccagtgagtgagaagagtgacccacagctcctcacatataagaatccagaggagag1020
gctgagctggttttcctctgcatctctgctgcgtgtca1058
<210>22
<211>720
<212>dna
<213>人工序列(artificialsequence)
<400>22
atggtgagcaagggcgaggagctgttcaccggggtggtgcccatcctggtcgagctggac60
ggcgacgtaaacggccacaagttcagcgtgtccggcgagggcgagggcgatgccacctac120
ggcaagctgaccctgaagttcatctgcaccaccggcaagctgcccgtgccctggcccacc180
ctcgtgaccaccctgacctacggcgtgcagtgcttcagccgctaccccgaccacatgaag240
cagcacgacttcttcaagtccgccatgcccgaaggctacgtccaggagcgcaccatcttc300
ttcaaggacgacggcaactacaagacccgcgccgaggtgaagttcgagggcgacaccctg360
gtgaaccgcatcgagctgaagggcatcgacttcaaggaggacggcaacatcctggggcac420
aagctggagtacaactacaacagccacaacgtctatatcatggccgacaagcagaagaac480
ggcatcaaggtgaacttcaagatccgccacaacatcgaggacggcagcgtgcagctcgcc540
gaccactaccagcagaacacccccatcggcgacggccccgtgctgctgcccgacaaccac600
tacctgagcacccagtccgccctgagcaaagaccccaacgagaagcgcgatcacatggtc660
ctgctggagttcgtgaccgccgccgggatcactctcggcatggacgagctgtacaagtaa720
<210>23
<211>34
<212>dna
<213>人工序列(artificialsequence)
<400>23
ataacttcgtatagcatacattatacgaagttat34
<210>24
<211>122
<212>dna
<213>人工序列(artificialsequence)
<400>24
aacttgtttattgcagcttataatggttacaaataaagcaatagcatcacaaatttcaca60
aataaagcatttttttcactgcattctagttgtggtttgtccaaactcatcaatgtatct120
ta122
<210>25
<211>1753
<212>dna
<213>人工序列(artificialsequence)
<400>25
gctcgctttcttgctgtccaatttctattaaaggttcctttgttccctaagtccaactac60
taaactgggggatattatgaagggccttgagcatctggattctgcctaataaaaaacatt120
tattttcattgcaatgatgtatttaaattatttctgaatattttactaaaaagggaatgt180
gggaggtcagtgcatttaaaacataaagaaatgaagagctagttcaaaccttgggaaaat240
acactatatcttaaactccatgaaagaaggtgaggctgcaaacagctaatgcacattggc300
aacagccctgatgcctatgccttattcatccctcagaaaaggattcaagtagaggcttga360
tttggaggttaaagttttgctatgctgtattttacattacttattgttttagctgtcctc420
atgaatgtcttttcactacccatttgcttatcctgcatctctcagccttgactccactca480
gttctcttgcttagagataccacctttcccctgaagtgttccttccatgttttacggcga540
gatggtttctcctcgcctggccactcagccttagttgtctctgttgtcttatagaggtct600
acttgaagaaggaaaaacagggggcatggtttgactgtcctgtgagcccttcttccctgc660
ctcccccactcacagtgacccggaatctgcagtgctagtctcccggaactatcactcttt720
cacagtctgctttggaaggactgggcttagtatgaaaagttaggactgagaagaatttga780
aagggggctttttgtagcttgatattcactactgtcttattaccctatcataggcccacc840
ccaaatggaagtcccattcttcctcaggatgtttaagattagcattcaggaagagatcag900
aggtctgctggctcccttatcatgtcccttatggtgcttctggctctgcagttattagca960
tagtgttaccatcaaccaccttaacttcatttttcttattcaatacctaggtaggtagat1020
gctagattctggaaataaaatatgagtctcaagtggtccttgtcctctctcccagtcaaa1080
ttctgaatctagttggcaagattctgaaatcaaggcatataatcagtaataagtgatgat1140
agaagggtatatagaagaattttattatatgagagggtgaaacctaaaatgaaatgaaat1200
cagacccttgtcttacaccataaacaaaaataaatttgaatgggttaaagaattaaacta1260
agacctaaaaccataaaaatttttaaagaaatcaaaagaagaaaattctaatattcatgt1320
tgcagccgttttttgaatttgatatgagaagcaaaggcaacaaaaggaaaaataaagaag1380
tgaggctacatcaaactaaaaaatttccacacaaaaaagaaaacaatgaacaaatgaaag1440
gtgaaccatgaaatggcatatttgcaaaccaaatatttcttaaatattttggttaatatc1500
caaaatatataagaaacacagatgattcaataacaaacaaaaaattaaaaataggaaaat1560
aaaaaaattaaaaagaagaaaatcctgccatttatgcgagaattgatgaacctggaggat1620
gtaaaactaagaaaaataagcctgacacaaaaagacaaatactacacaaccttgctcata1680
tgtgaaacataaaaaagtcactctcatggaaacagacagtagaggtatggtttccagggg1740
ttgggggtgggag1753
<210>26
<211>225
<212>dna
<213>人工序列(artificialsequence)
<400>26
ctgtgccttctagttgccagccatctgttgtttgcccctcccccgtgccttccttgaccc60
tggaaggtgccactcccactgtcctttcctaataaaatgaggaaattgcatcgcattgtc120
tgagtaggtgtcattctattctggggggtggggtggggcaggacagcaagggggaggatt180
gggaagacaatagcaggcatgctggggatgcggtgggctctatgg225
<210>27
<211>1032
<212>dna
<213>人工序列(artificialsequence)
<400>27
atgtccaatcttctaaccgtccaccaaaatctacctgctctgcctgtggatgctacatct60
gatgaggtgagaaagaacctgatggacatgttcagagacagacaggctttctctgagcac120
acatggaagatgctgctgtctgtctgcaggagctgggctgcttggtgtaagctgaacaac180
agaaagtggttccctgctgagcctgaggatgtgagagactacctgctgtacctccaggct240
agaggactggctgtgaagacaatccagcagcacctgggacagctgaacatgctgcacaga300
aggtctggactgcctagaccttctgacagcaatgctgtgagcctggtgatgagaagaatc360
agaaaggagaatgtggatgctggagagagagctaagcaggctctggcttttgagagaaca420
gactttgaccaggtgagaagcctgatggagaactctgacagatgtcaggacatcagaaac480
ctggctttcctgggaattgcttacaacacactgctgagaattgctgagattgctagaatc540
agagtgaaggacatcagcagaacagatggaggaagaatgctgatccacattggaagaaca600
aagacactggtgagcacagctggagtggagaaggctctgagcctgggagtgacaaagctg660
gtggagagatggatctctgtgtctggagtggctgatgaccctaacaactacctgttctgt720
agagtgagaaagaatggagtggctgctccttctgctacaagccagctgagcacaagggct780
ctggagggaatctttgaggctacacacagactgatctatggagctaaggatgactctgga840
cagagatacctggcttggtctggacactctgctagagtgggagctgctagagacatggct900
agagctggagtgagcatccctgagatcatgcaggctggaggatggacaaatgtgaacatt960
gtgatgaactacatcagaaacctggactctgagacaggagctatggtgagactgctggag1020
gatggagactaa1032
<210>28
<211>587
<212>dna
<213>人工序列(artificialsequence)
<400>28
cccctctccctcccccccccctaacgttactggccgaagccgcttggaataaggccggtg60
tgcgtttgtctatatgttattttccaccatattgccgtcttttggcaatgtgagggcccg120
gaaacctggccctgtcttcttgacgagcattcctaggggtctttcccctctcgccaaagg180
aatgcaaggtctgttgaatgtcgtgaaggaagcagttcctctggaagcttcttgaagaca240
aacaacgtctgtagcgaccctttgcaggcagcggaaccccccacctggcgacaggtgcct300
ctgcggccaaaagccacgtgtataagatacacctgcaaaggcggcacaaccccagtgcca360
cgttgtgagttggatagttgtggaaagagtcaaatggctctcctcaagcgtattcaacaa420
ggggctgaaggatgcccagaaggtaccccattgtatgggatctgatctggggcctcggtg480
cacatgctttacatgtgtttagtcgaggttaaaaaaacgtctaggccccccgaaccacgg540
ggacgtggttttcctttgaaaaacacgatgataatatggccacaacc587
- 还没有人留言评论。精彩留言会获得点赞!