一种免标记荧光检测基因的方法及试剂盒与流程
本发明属于分析检测领域,具体涉及一种免标记荧光检测基因的方法及试剂盒。
背景技术:
微生物、病毒的基因检测是常见的鉴定方法,在疾病诊断、微生物鉴定、检验检疫等方面有着非常广泛的应用,具有非常重要的意义。
传统的基因检测方法有聚合酶链式反应,酶联免疫吸附和免疫印迹等方法。这些方法需要分离富集、操作繁琐和费时,不利于快速现场检测。近年来,利用生物传感器检测病毒的方法备受关注,已建立荧光、电化学以及比色法等分析技术,但大多需要进行标记,因而限制了这些技术的广泛应用。
开发出一种检测过程快速、操作简单、免标记和灵敏度高,从而降低成本,易于推广具有非常重要的意义。
技术实现要素:
本发明的目的在于克服现有技术的不足,提供一种免标记荧光检测基因的方法及试剂盒。
本发明所采取的技术方案是:
一种免标记荧光检测基因的试剂盒,包括反应缓冲液、与g-quadruplex结合后荧光发生变化的荧光染料,还包括核酸探针ls、ss、hs和fs,其中:
核酸探针ls从5'端开始依次为i、ⅱ和ⅲ区域,其中i区包含链置换反应的支点序列,能通过碱基互补识别待测基因;ⅱ区与hs核酸探针完全互补;ⅲ区与核酸探针ss的ⅲ*区互补,使得核酸探针ss上的g-quadruplex序列被绑定;
核酸探针ss从5'端开始依次为ⅲ*和ⅳ区域,其中ⅲ*区与核酸探针的ⅲ区互补,ⅲ*和ⅳ区共同构成g-quadruplex序列;
核酸探针fs从5'端开始依次为ⅲ*和ⅱ*区域,其中ⅲ*和ⅱ*区分别与核酸探针ls的ⅲ和ⅱ区完全互补。
作为上述试剂盒的进一步改进,核酸探针ls中i区独立包含6~8个碱基,ⅱ区独立包含12~19个碱基,ⅲ区独立包含10~18个碱基。
作为上述试剂盒的进一步改进,核酸探针ss中的ⅳ区包含7~8个碱基。
作为上述试剂盒的进一步改进,核酸探针ls中,ⅱ区的序列为:aaataaaatagtaaagaga,ⅲ区的序列为:gccctacccaatctgtgc。
作为上述试剂盒的进一步改进,核酸探针ss的ⅳ区序列为:gggttggg。
作为上述试剂盒的进一步改进,待测基因为hiv-1;
核酸探针ls的序列为:5'-ctgggatt-aaataaaatagtaaagaga-gccctacccaatctgtgc-3';
核酸探针ss的序列为:5'-gcacagattgggtagggc-gggttggg-3';
核酸探针hs的序列为:5'-tctctttactattttattt-3';
核酸探针fs的序列为:5'-gcacagattgggtagggctctctttactattttattt-3'。
作为上述试剂盒的进一步改进,缓冲液包括tris-hcl缓冲液、pbs缓冲液、hepes缓冲液。
作为上述试剂盒的进一步改进,荧光染料选自n-甲基卟啉二丙酸ix(nmm)、四(二异丙基胍基)酞氰锌(zn-digp)、原卟啉(ppix)。
一种基因检测方法,包括如下步骤:
1)提取待测样品的核酸序列,得到待测溶液;
2)将核酸探针ls、ss和hs混合并使其自然配对形成稳定的底物探针sp;
3)将待测溶液、底物探针sp和核酸探针fs混合,反应完全后入荧光染料,测定其初始荧光值;
4)进一步反应完全后,测量反应后的荧光值;
5)根据荧光值的变化情况确定待测基因的量;
其中,核酸探针ls、ss、hs和fs如上所述。
作为上述方法的进一步改进,核酸探针ls、ss和hs以1:1:1的摩尔比混合,以减少游离单链核酸序列的存在。优选的,通过加热的然后自然冷却的方式使核酸探针ls、ss和hs自然配对。
作为上述方法的进一步改进,将核酸探针ls、ss和hs按照1:1:1的比例混合,然后置于95℃的水浴锅中加热7分钟,随后缓慢冷却至室温,最终形成浓度为10μm的稳定的底物探针sp;
将2μl待测溶液与含有300nm底物探针sp和300nm核酸探针fs溶液混合,反应体系为50μl,室温下反应120分钟。
本发明的有益效果是:
本发明以底物探针sp结合核酸探针fs辅助目标信号级联再循环扩增策略。以g-quadruplex为信号报告分子,可现实免标记检测基因,简化了操作,降低了成本。整个检测过程响应迅速,无需专业训练即可掌握操作流程,便于快速推广使用。
本发明所述的检测方法和试剂盒,检测度灵敏高,检测限低,精密度高,特异性高。
附图说明
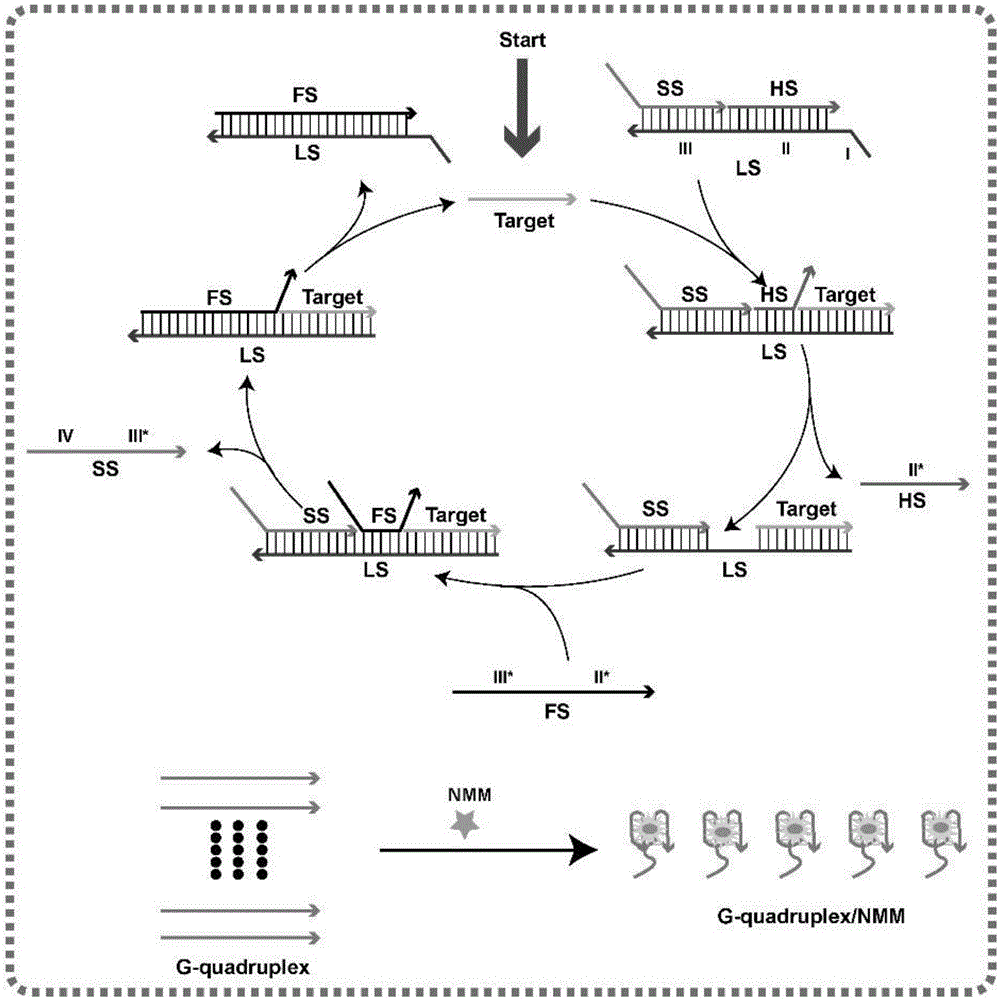
图1是本发明的检测反应原理图;
图2是不同浓度的hiv-1基因检测的结果图;
图3是hiv-1基因检测的特异性实验结果图。
具体实施方式
一种免标记荧光检测基因的试剂盒,包括反应缓冲液、与g-quadruplex结合后荧光发生变化的荧光染料,还包括核酸探针ls、ss、hs和fs,其中:
核酸探针ls从5'端开始依次为i、ⅱ和ⅲ区域,其中i区包含链置换反应的支点序列,能通过碱基互补识别待测基因;ⅱ区与hs核酸探针完全互补;ⅲ区与核酸探针ss的ⅲ*区互补,使得核酸探针ss上的g-quadruplex序列被绑定;
核酸探针ss从5'端开始依次为ⅲ*和ⅳ区域,其中ⅲ*区与核酸探针的ⅲ区互补,ⅲ*和ⅳ区共同构成g-quadruplex序列;
核酸探针fs从5'端开始依次为ⅲ*和ⅱ*区域,其中ⅲ*和ⅱ*区分别与核酸探针ls的ⅲ和ⅱ区完全互补。
各探针的各区的长度可以根据链置换反应碱基设计原则和成本原则确定。如i区是根据链置换反应支点序列设计原理,支点一般为6~8个碱基;ii取选取的原则是根据两条核酸链碱基互补配对形成双链的稳定性角度和成本的角度来设计碱基个数的;iii和iv区是根据两条核酸链碱基互补配对形成双链的稳定性角度,成本的角度和g-quadruplex序列被绑住一半以减小体系信号背景的角度来设计碱基个数。因此,作为上述试剂盒的进一步改进,核酸探针ls中i区独立包含6~8个碱基,ⅱ区独立包含12~19个碱基,ⅲ区独立包含10~18个碱基。
作为上述试剂盒的进一步改进,核酸探针ss中的ⅳ区包含7~8个碱基。
作为上述试剂盒的进一步改进,核酸探针ls中,ⅱ区的序列为:aaataaaatagtaaagaga(seqidno:1),ⅲ区的序列为:gccctacccaatctgtgc(seqidno:2)。
作为上述试剂盒的进一步改进,核酸探针ss的ⅳ区序列为:gggttggg(seqidno:3)。
作为上述试剂盒的进一步改进,待测基因为hiv-1;
核酸探针ls的序列为:5'-ctgggatt-aaataaaatagtaaagaga-gccctacccaatctgtgc-3'(seqidno:4);
核酸探针ss的序列为:5'-gcacagattgggtagggc-gggttggg-3'(seqidno:5);
核酸探针hs的序列为:5'-tctctttactattttattt-3'(seqidno:6);
核酸探针fs的序列为:5'-gcacagattgggtagggctctctttactattttattt-3'(seqidno:7)。
作为上述试剂盒的进一步改进,缓冲液包括tris-hcl缓冲液、pbs缓冲液、hepes缓冲液。
作为上述试剂盒的进一步改进,荧光染料选自n-甲基卟啉二丙酸ix(nmm)、四(二异丙基胍基)酞氰锌(zn-digp)、原卟啉(ppix)。
一种基因检测方法,包括如下步骤:
1)提取待测样品的核酸序列,得到待测溶液;
2)将核酸探针ls、ss和hs混合并使其自然配对形成稳定的底物探针sp;
3)将待测溶液、底物探针sp和核酸探针fs混合,反应完全后入荧光染料,测定其初始荧光值;
4)进一步反应完全后,测量反应后的荧光值;
5)根据荧光值的变化情况确定待测基因的量;
其中,核酸探针ls、ss、hs和fs如上所述。
作为上述方法的进一步改进,核酸探针ls、ss和hs以1:1:1的摩尔比混合,以减少游离单链核酸序列的存在。优选的,通过加热的然后自然冷却的方式使核酸探针ls、ss和hs自然配对。
作为上述方法的进一步改进,将核酸探针ls、ss和hs按照1:1:1的比例混合,然后置于95℃的水浴锅中加热7分钟,随后缓慢冷却至室温,最终形成浓度为10μm的稳定的底物探针sp;
将2μl待测溶液与含有300nm底物探针sp和300nm核酸探针fs溶液混合,反应体系为50μl,室温下反应120分钟。
本发明的反应原理如图1所示:
1)核酸探针ls、ss和hs混合并互补配对形成稳定的底物探针sp;
2)当待测基因存在时,底物探针sp的i区和ⅱ区与待测基因通过碱基互补结合,使核酸探针hs从底物探针sp中被释放出来;当待测基因不存在时,底物探针sp保持不变,后续反应无法进行;
3)核酸探针hs的释放,使得核酸探针ls中间支点的暴露,接着核酸探针fs利用暴露的支点发生链置换反应,使得核酸探针ss和待测基因从底物探针中被释放出来;
4)被释放的目标基因待测,又可与剩下的底物探针sp发生链置换反应;
5)在目标基因待测的不断循环下,释放出大量的核酸探针ss。不断产生的核酸探针ss可形成g-quadruplex;
6)g-quadruplex能与荧光染料nmm结合(λex=399nm,λem=610nm;λex为激发光波长,λem为发射光波长峰值),产生明显的荧光变化,根据释放的g-quadruplex/nmm复合物浓度与荧光强度成线性关系(λex=399nm,λem=610nm),从而达到检测待测基因的目的。
以hiv-1基因的检测为例,在最佳条件下,该方法的线性范围从10pm到1μm,检测限为1.9pm。该方法还对其他可能的干扰核酸表现出显著的选择性。血清实际样品分析hiv-1基因的结果表明,该方法具有较好的精密度和准确度。
荧光染料只要能与g-quadruplex复合并会引起荧光变化即可,这些荧光染料包括nmm等。
缓冲溶液是模拟生理条件,有利于碱基配对。缓冲液的成分、种类和ph可以适应性调整。优选的,缓冲溶液包括tris-hcl缓冲溶液、pbs缓冲液、hepes缓冲液等,ph=7.0-7.5。进一步的,缓冲溶液为20mmtris-hcl缓冲溶液,其中含有100mmnacl,10mmmgcl2,15mmkcl,ph=7.4。
下面结合实施例对本发明做进一步的说明,但不局限于此。
实施例1
一种免标记荧光检测hiv-1基因的试剂盒,包括下列成分:
(1)核酸探针ls、ss、hs和fs,序列分别如下:
ls:5'-ctgggatt(i区)-aaataaaatagtaaagaga(ⅱ区)-gccctacccaatctgtgc(ⅲ区)-3';
ss:5'-gcacagattgggtagggc(ⅲ*区)-gggttggg(ⅳ区)-3';
hs:5'-tctctttactattttattt(ⅱ*区)-3';
fs:5'-gcacagattgggtagggc(ⅲ*区)-tctctttactattttattt(ⅱ*区)-3'。
(2)20mmtris-hcl缓冲溶液,其中含有100mmnacl,10mmmgcl2,15mmkcl,ph=7.4。
一种免标记荧光检测hiv-1基因的方法,按照如下步骤进行:
a.底物探针sp的形成:
将核酸探针ls、ss和hs按照1:1:1的比例混合,然后置于95℃的水浴锅中加热7分钟,随后缓慢冷却至室温,最终形成浓度为10μm的稳定的底物探针sp;
b.hiv-1基因的检测:
1)将2μl待测溶液加入在含有300nm底物探针sp和300nm核酸探针fs,反应体系为50μl,室温下反应120分钟;
2)加入1μmnmm荧光染料,室温下接着反应30分钟;
3)把反应后的溶液稀释到200μl,根据释放的g-quadruplex/nmm复合物浓度与荧光强度成线性关系(λex=399nm,λem=610nm),从而达到检测hiv-1基因的目的。
不同浓度hiv-1基因的检测:
配制hiv-1基因标准溶液,浓度分别为0、10pm、102pm、103pm、104pm、105pm和106pm,4℃保存。
将不同浓度的hiv-1基因溶液分别加到实施例1中所述的反应体系中,充分反应后观察体系荧光强度变化,如图2(图2a:在λex=399nm条件下,不同hiv-1基因浓度所对应的发射光波谱图;图2b:在λex=399nm条件下,λem=610nm得到的荧光标准曲线图;图2c:荧光强度与hiv-1基因浓度的对数之间的线性关系)所示,10pm的hiv-1基因可产生明显的荧光变化,说明其检测限<10pm。随着hiv-1基因浓度增加,荧光强度也增加,并逐渐趋于饱和。
特异性实验:
配制100nm不同核酸的标准溶液,它们分别是m1,m2,m3和nc。
m1:5’-gctatacattcttactattttatttaatcgcag-3’(seqidno:8)
m2:5’-gctatacattcttactattttatttaatggcag-3’(seqidno:9)
m3:5’-gctatacattcttactattttattaaatggcag-3’(seqidno:10)
nc:5’-tgccgctcatccgccacataaaatggcaggcta-3’(seqidno:11)
其中下划线字母代表错配碱基。
将100nm的不同干扰物标准溶液和100nmhiv-1基因溶液分别加到实施例1中所述的反应体系中,充分反应后观察体系荧光变化,如图3所示,100nm的m1、m2、m3和nc荧光强度均远远低于100nm的hiv-1基因,其中m1体系和m2的荧光强度分别为hiv-1基因的34%和32%。m3体系和nc的荧光强度与空白组一样。这证明该方法对hiv-1基因的检测具有较好的特异性。
其他基因的检测,可以参照实施例1的方法进行,适应性替换待测基因识别序列即可。
上述实施例为本发明较佳的实施方式,但本发明的实施方式并不受上述实施例的限制,其他的任何未背离本发明的精神实质与原理下所作的改变、修饰、替代、组合、简化,均应为等效的置换方式,都包含在本发明的保护范围之内。
sequencelisting
<110>广东省生态环境技术研究所
<120>一种免标记荧光检测基因的方法及试剂盒
<130>
<160>11
<170>patentinversion3.5
<210>1
<211>19
<212>dna
<213>人工序列
<400>1
aaataaaatagtaaagaga19
<210>2
<211>18
<212>dna
<213>人工序列
<400>2
gccctacccaatctgtgc18
<210>3
<211>8
<212>dna
<213>人工序列
<400>3
gggttggg8
<210>4
<211>45
<212>dna
<213>人工序列
<400>4
ctgggattaaataaaatagtaaagagagccctacccaatctgtgc45
<210>5
<211>26
<212>dna
<213>人工序列
<400>5
gcacagattgggtagggcgggttggg26
<210>6
<211>19
<212>dna
<213>人工序列
<400>6
tctctttactattttattt19
<210>7
<211>37
<212>dna
<213>人工序列
<400>7
gcacagattgggtagggctctctttactattttattt37
<210>8
<211>33
<212>dna
<213>人工序列
<400>8
gctatacattcttactattttatttaatcgcag33
<210>9
<211>33
<212>dna
<213>人工序列
<400>9
gctatacattcttactattttatttaatggcag33
<210>10
<211>33
<212>dna
<213>人工序列
<400>10
gctatacattcttactattttattaaatggcag33
<210>11
<211>33
<212>dna
<213>人工序列
<400>11
tgccgctcatccgccacataaaatggcaggcta33
- 还没有人留言评论。精彩留言会获得点赞!