鉴别人甲状腺结节良恶性的试剂盒及其使用方法和应用与流程
本发明属于试剂盒技术领域,特别涉及鉴别人甲状腺结节良恶性的试剂盒及其使用方法和应用。
背景技术:
甲状腺结节(thyroidnodule)是人群中普遍存在的一种甲状腺疾病,多数结节是良性的,可以采取保守治疗,但有5%-10%的甲状腺结节是恶性的,需要早期手术治疗,才能获得良好的预后。如果给予大量不需要手术的甲状腺良性结节患者手术治疗,将会产生巨大的医保负担;反之,如果不能从大量甲状腺良性结节中识别鉴定真正的恶性肿瘤,则延缓对这些患者的治疗,危及患者的生命健康。因此,及时准确的检测甲状腺结节的良恶性是至关重要的。
随着分子生物学技术的进展,分子诊断在甲状腺结节良恶性的鉴别诊断中,逐渐受到人们的关注。结节良恶性分子鉴别诊断的理论基础是基于有些甲状腺癌的致病基因,只在癌症患者的癌组织中发生特异性的体细胞突变或融合基因的出现,这种突变或新融合基因在患者的正常甲状腺细胞及非甲状腺癌患者的甲状腺组织中是不存在的。因此,以这些致病基因作为分子标志,在甲状腺癌的良恶性鉴别鉴别诊断中,具有特异性。
其中,braf基因上第600位氨基酸的val600glu突变的甲状腺结节100%的病人是恶性结节,虽然这些基因突变在甲状腺结节良恶性鉴别诊断中有非常好的特异性,但每一致病基因在甲状腺癌病人中的突变频率是不定的,因此,单靠这样对单个基因的分子突变进行检测,对阳性患者虽然有重要的鉴定意义,但对阴性患者存在漏诊的可能,耽误患者的治疗。因此要解决甲状腺癌分子诊断这一困境,需要对导致甲状腺癌的多个基因同时进行突变检测,才能够提高甲状腺结节良恶性鉴别诊断的特异性,降低假阴性率。
但是,想要在甲状腺结节样本中,同时进行多个甲状腺癌特异性致病基因的体细胞突变检测,需要突破以下几个方面的科学和技术难点:首先,虽然现有文献报道大量的甲状腺癌的致病基因突变,但在这些报道的突变基因中,哪些是真正的致病基因是不清楚的。其次,在目前报道的甲状腺癌致病基因中,哪些基因的组合在甲状腺结节鉴别诊断中阳性率高以及阴性漏诊可能性小也是不知道的。因此,找到这样的一群甲状腺癌致病基因的组合,将其应用于甲状腺结节良恶性鉴别中以降低错误、误判的概率,是非常重要的。
技术实现要素:
针对现有技术存在的不足,本发明的第一个目的在于提供一种鉴别人甲状腺结节良恶性的试剂盒,其基于甲状腺癌的致病基因只存在于癌症患者发生特异性体细胞突变的组织中这一特点,测定braf基因、kras基因、nras基因、hras基因及tert基因上的突变位点,为鉴别甲状腺结节的良恶性提供了良好的辅助作用。
本发明的第二个目的在于提供一种鉴别人甲状腺结节良恶性的试剂盒的使用方法,其通过两轮pcr扩增,即便甲状腺结节的样本量较少,依旧能够正常扩增出目的基因。
本发明的第三个目的在于提供一种鉴别人甲状腺结节良恶性的试剂盒的应用,该试剂盒能够为临床诊断甲状腺结节的良恶性以及判断预后提供辅助作用。
为实现上述目的,本发明提供了如下技术方案:
一种鉴别人甲状腺结节良恶性的试剂盒,其特征在于,所述试剂盒包括pcr缓冲液体系、测序引物体系、taq酶、ung酶以及阴性质控品;
所述pcr缓冲液体系由pcr缓冲液1、pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液6和pcr缓冲液7组成,且pcr缓冲液1包括引物对braf-1、引物对kras-1、引物对nras-1、引物对hras-1、引物对hras-2和引物对tert-1,pcr缓冲液2包括引物对braf-2,pcr缓冲液3包括引物对kras-2,pcr缓冲液4包括引物对nras-2,pcr缓冲液5包括引物对hras-3,pcr缓冲液6包括引物对hras-4,pcr缓冲液7包括引物对tert-2;
所述测序引物体系包括测定braf基因、kras基因、nras基因、hras基因及tert基因上19个突变位点的引物对braf-2、引物对kras-2、引物对nras-2、引物对hras-3、引物对hras-4和引物对tert-2;
所述19种突变位点依次为:braf基因的t1799a和a1801g,kras基因的g34a、g34t、g35a、g35t、g37c、g37t和g38a,nras基因的c181a、a182g、a182t、a183t和a183c,hras基因的g35t、c181a和a182g,tert基因的c250t和c228t。
进一步地,braf-1如seqidno.26和seqidno.27所示,braf-2如seqidno.28和seqidno.29所示,kras-1如seqidno.30和seqidno.31所示,kras-2如seqidno.32和seqidno.33所示,nras-1如seqidno.34和seqidno.35所示,nras-2如seqidno.36和seqidno.37所示,hras-1如seqidno.38和seqidno.38所示,hras-2如seqidno.40和seqidno.41所示,hras-3如seqidno.42和seqidno.43所示,hras-4如seqidno.44和seqidno.45所示,tert-1如seqidno.46和seqidno.47所示,tert-2如seqidno.48和seqidno.49所示。
进一步地,所述pcr缓冲液1、pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液6和pcr缓冲液7均还包括有pcrbuffer、dntp或dutp、无核酸酶水。
进一步地,所述pcrbuffer的浓度为10×。
进一步地,所述dntp的浓度为10mm-20mm。
进一步地,所述pcr缓冲液1、pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液6和pcr缓冲液7均还包括有q-solution。
进一步地,所述试剂盒的保存温度为-20℃。
为实现上述第二个目的,本发明提供了如下技术方案:
一种鉴别人甲状腺结节良恶性的试剂盒的使用方法,包括以下步骤:
①、pcr扩增
①-1、第一轮pcr反应体系:待测样本dna1/阴性质控品,1-5μl;pcr缓冲液1,14-18μl;ung酶,0.5μl;taq酶0.5μl;
①-2、第二轮pcr反应体系:待测样本dna2/阴性质控品,1-5μl,pcr缓冲液2/3/4/5/6/7,14-18μl,taq酶,0.5μl;
其中,待测样本dna1为甲状腺结节的样本dna,且dna的含量为20-100ng;待测样本dna2为第一轮pcr产物用阴性质控品稀释10倍所得;
②、pcr产物电泳鉴定
取步骤①-2中使用pcr缓冲液2-pcr缓冲液7处理得到的pcr产物,依次对其进行上样跑胶,得到电泳图,若电泳图中的跑胶带清晰明亮则表示pcr扩增正常;
③、pcr产物测序
取经步骤②鉴定pcr扩增正常的pcr产物,对应使用引物对braf-2、引物对kras-2、引物对nras-2、引物对hras-3、引物对hras-4和引物对tert-2进行一代测序。
进一步地,第一轮pcr反应条件为:
第二轮pcr反应条件为:
为实现上述第三个目的,本发明提供了如下技术方案:
一种鉴别人甲状腺结节良恶性的试剂盒的应用,所述试剂盒为临床诊断甲状腺结节的良恶性以及判断预后提供辅助作用。
本发明具有以下有益效果:
1、本发明选择braf基因、kras基因、nras基因、hras基因及tert基因的突变位点设置相应的引物,实现同时检测多种基因变异,为鉴别甲状腺结节的良恶性提供了良好的辅助作用,采用一代测序的手段,使得检测变得简单、容易操作;
2、本发明通过两轮pcr反应,即便是甲状腺结节的样本量较少,依旧能够正常扩增出目的基因;
3、本发明能够为临床诊断甲状腺结节的良恶性以及判断预后提供辅助作用,有效降低了错判、误判的概率。
附图说明
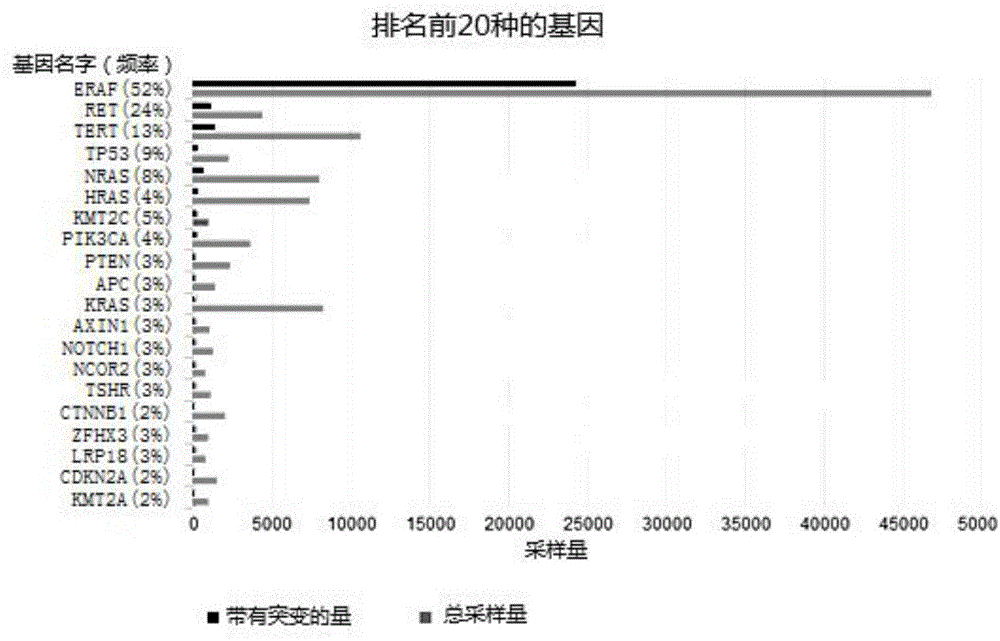
图1为cosmic数据库里甲状腺癌常见的突变基因的分析图;
图2为实施例1的电泳图;
图3为实施例2的电泳图;
图4为实施例3的电泳图;
图5为实施例4的电泳图。
图中,图2至图5中编号1-8的跑胶带分别指代为:braf基因、kras基因、nras基因、tert基因、hras基因1、hras基因2的pcr产物、阴性对照pcr产物以及marker。
具体实施方式
以下结合具体附图对本发明作进一步详细说明。
1、突变基因的分析及选择
在本领域中,cosmic数据库里甲状腺癌常见的突变基因参见图1,其中,braf基因、ret基因、ras基因家族和tert基因位于前列。
braf基因编码丝氨酸-苏氨酸激酶,其由ras蛋白激活并转运结合到质膜后可以改变细胞的位置。若braf基因发生突变,其便会被持续激活,引起mek/rek信号转导的紊乱,导致细胞过度增值,出现恶性转化。该rraf基因与淋巴结转移、甲状腺外扩散、癌症晚期(ⅲ期和ⅳ期)、癌症复发等密切相关。
ret基因在甲状腺髓样癌种与种系或者体细胞突变最为密切,而甲状腺乳头状癌也可能在第10号染色体上存在隐匿ret/ptc1及ptc3的基因重排,ret/ptc基因变异与因年龄或辐射暴露所患的癌症相关,在预后方面与淋巴结转移相关,但对于变异和肿瘤的低分化或未分化不相关。
kras基因、nras基因、hras基因均属于ras基因,其与信号传到关系密切,介导酪氨酸激酶到g蛋白欧联受体到mapk和pi3k-akt效应器的信号通路,调节细胞的分化、增殖和凋亡。ras基因的突变可以使其与gtp(密码子12、13)的关系更加密切,或抑制自动催化的gtpase(密码子61)的功能。这两种机制都会持续、异常地激活下游的mapk和pi3/akt信号通路,继而导致肿瘤的发生。ras基因在甲状腺良恶性肿瘤中都存在,且与肿瘤惰性及侵袭性临床病程相关,可作为癌细胞亚型的一个标记,显示形态学分化良好但已有潜在转移及去分化的癌灶。
tert为端粒酶逆转录酶,是指端粒酶中具有逆转录酶活性的催化亚基,属于端粒酶的一部分,而端粒酶能够讲dna复制损失的端粒进行修复延长,使得细胞分裂的次数增加。tert基因的突变是近年来发现的一种肿瘤分子标志物,其突变主要集中在启动子区的c250t和c228t两个位点,突变概率达70%-80%。由于tert基因的突变在启动子区,因此使得tert启动子的活性增加,导致细胞过度增值,促使突变基因的扩增,加剧甲状腺癌的病情。
另外,经研究发现,携带tert突变基因(c250t,c228t)和brafv600e突变基因的患者预后不良,而brafv600e基因突变和tert基因突变又与甲状腺乳头状癌(ptc)的高死亡率(易转移性、癌症复发后放射碘亲和力缺失)密切相关,具体的ptc特异性死亡风险顺序为合并双基因突变﹥﹥单brafv600e基因突变=单tert基因突变﹥两基因均无突变,如下表一所示,在调整各因素后,合并双基因突变的死亡风险仍为两基因均无突变的9倍左右。
表一每1000人/年ptc特异性死亡率和不同基因组的危险率
综上可得,braf基因、tert基因以及ras基因家族的突变是甲状腺癌最为关键的致病基因,若是该基因的组合中有任意一个出现突变,则判定甲状腺结节的待测样本为恶性,若该基因的组合均无发生突变,则说明该甲状腺结节为恶性的可能性较小,以此为鉴别甲状腺结节的良恶性提供了良好的辅助作用。
由此,本发明的试剂盒选择braf基因、ras基因、nras基因、hras基因及tert基因的突变位点作为分子标志,以此设置对应的测序引物,实现同时检测多种基因变异,使得本试剂盒的组合具有优良的特异性,降低了错判、误判的概率。
2、实施例
以下结合具体实施方式对本发明作进一步详细说明。
需要说明的是,本发明公开的用于鉴别人甲状腺结节良恶性的试剂盒,供二十四人份甲状腺结节的测定,包括测序引物体系、pcr缓冲液体系、taq酶、ung酶以及阴性质控品;pcr缓冲液体系由pcr缓冲液1、pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液6和pcr缓冲液7组成;
pcr缓冲液1包括引物对braf-1、引物对kras-1、引物对nras-1、引物对hras-1、引物对hras-2和引物对tert-1;
pcr缓冲液2包括引物对braf-2,pcr缓冲液3包括引物对kras-2,pcr缓冲液4包括引物对nras-2,pcr缓冲液5包括引物对hras-3,pcr缓冲液6包括引物对hras-4,pcr缓冲液7包括引物对tert-2;
其中,测序引物系列包括测定braf基因、kras基因、nras基因、hras基因及tert基因上19个突变位点的引物对braf-2、引物对kras-2、引物对nras-2、引物对hras-3、引物对hras-4和引物对tert-2,且该测序引物系列中的各引物对与pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液6和pcr缓冲液7中的引物对一致。本发明的试剂盒保存于在-20℃的环境中,以保证各试剂优良的性能。
19种突变位点依次为:braf基因的t1799a和a1801g,kras基因的g34a、g34t、g35a、g35t、g37c、g37t和g38a,nras基因的c181a、a182g、a182t、a183t和a183c,hras基因的g35t、c181a和a182g,tert基因的c250t和c228t,该5种基因的野生型和突变型的基因序列分析如下表二,各测序引物对的序列如下表三,且下述引物对均委外进行合成。
表二五种基因的野生型和突变型的基因序列分析表
表三五种基因的测序引物对的序列表
另外,pcr缓冲液1、pcr缓冲液2、pcr缓冲液3、pcr缓冲液4、pcr缓冲液5、pcr缓冲液和pcr缓冲液7均还包括有pcrbuffer、dntp或dutp、无核酸酶水和q-solution,且pcrbuffer、dntp、dutp、q-solution均从市面上购买获得。pcrbuffer的浓度优选为10×,除此之外还可以为其他浓度;dntp的浓度优选为10mm-20mm,除此之外还可其他浓度;q-solution浓度优选为5×,除此之外还可其他浓度;无核酸酶水为实验室自制的灭菌双蒸水。
本发明中的甲状腺结节的样本主要为甲状腺穿刺样本、新鲜病理组织、术后冰冻组织和石蜡包埋组织,除此之外还可以为其他形式的样本,其获得渠道为医院经病理分析后剩余的组织样本。
1.1、实施例1
一种鉴别人甲状腺结节良恶性的试剂盒的使用方法,包括pcr扩增、pcr产物电泳鉴定、pcr产物测序的操作步骤。
①、pcr扩增:
该试剂盒的组分和含量按表四的pcr反应体系于冰上进行配置。
表四pcr反应体系
其中,待测样本dna1为甲状腺结节的样本dna,具体为经病理分析后判定为良性甲状腺结节的穿刺样本,该样本dna使用sigma公司出售的细胞dna提取试剂盒提取获得,dna的含量为20ng;阴性质控品为经高压灭菌所得的无核酸酶水,每种样本dna均对应设置有一阴性对照组;待测样本dna2为第一轮pcr产物用阴性质控品稀释10倍所得;pcr缓冲液1-pcr缓冲液7的组分及含量参见表五;该试剂盒的反应条件如下表六所示。
表五pcr缓冲液1-pcr缓冲液7的组分及含量
表六pcr反应条件
②、pcr产物电泳鉴定
②-1、配置tae:将浓度为50×的tae储存液于4℃保存,取100ml储存液配置成5l浓度为1×的tae工作液,备用;
②-2、制胶:将1.4g的agarose粉末溶于120ml的1×tae工作液中,微波炉高火2-3min溶解,待液体温度降至约为60℃,按体积比为10000:1加入12μl的gel-red,充分混匀,灌胶;
②-3、制备上样:
a、上样6×loadingbuffer,用1×tae工作液稀释,且loadingbuffer和tae工作液的体积比为1:2,得到loadingbuffer稀释液;
b、分别取2μl步骤①中使用pcr缓冲液2-pcr缓冲液7处理得到的pcr产物,以及6份1μl步骤②-3中制得的loadingbuffer稀释液,每份pcr产物对应一份loadingbuffer稀释液,两两混匀后形成6份样品,依次对其上样跑胶;
c、上样顺序为:braf基因的pcr产物、kras基因的pcr产物、nras基因的pcr产物、tert基因的pcr产物、hras基因1的pcr产物、hras基因2的pcr产物、阴性对照pcr产物,依次编号为1-7;第8泳道上3μl在4℃保存的marker(2000bp);
②-4、电泳:黑色接口端接负极,红色接口端接正极,120v电泳15-20min,获得如图2所示的电泳图,电泳图中各基因片段的跑胶带明亮清晰;
由图2可得,本实施中能够较好的将braf基因、kras基因、nras基因、hras基因1、hras基因2以及tert基因的突变位点进行有效扩增,扩增长度为100-200bp,且阴性对照物无扩增,可对该基因片段进行后续的测序操作。
③、pcr产物测序
取步骤①中使用pcr缓冲液2至pcr缓冲液7处理得到的pcr产物,对应使用braf-2、kras-2、nras-2、hras-3、hras-4和tert-2进行一代测序,测得的基因序列与表三中的基因序列进行比较。
经测序得到:nras基因在a182g上发生了突变,tert基因在c250t上发生了突变;另外,braf基因、kras基因、hras基因1以及hras基因2均为野生型,因此该甲状腺结节应为恶性而非良性,以此便于患者和医生及时做出相应的治疗方案。
1.2、实施例2
与实施例1的不同之处在于,pcr反应体系如下表七所示,pcr缓冲液1-pcr缓冲液7的组分及含量如下表八所示,甲状腺结节的样本dna具体为经病理分析后判定为良性甲状腺结节的新鲜病理组织,dna的含量为40ng,其被测对象为同一个患者,其电泳图如图3所示,电泳图中各基因片段的跑胶带明亮清晰,但比实施例1模糊一点,其电泳图与实施例1的基本一致,测得的基因序列也与实施例1相同。
表七pcr反应体系
表八pcr缓冲液1-pcr缓冲液7的组分及含量
1.3、实施例3
与实施例1的不同之处在于,pcr反应体系如下表九所示,pcr缓冲液1-pcr缓冲液7的组分及含量如下表十所示,甲状腺结节的样本dna具体为经病理分析后判定为良性甲状腺结节的术后冰冻组织,dna的含量为100ng,其被测对象为同一个患者,其电泳图如图4所示,电泳图中各基因片段的跑胶带明亮清晰,且其电泳图与实施例1的基本一致,测得的基因序列也与实施例1的相同。
表九pcr反应体系
表十pcr缓冲液1-pcr缓冲液7的组分及含量
1.4、实施例4
与实施例1的不同之处在于,pcr反应体系如下表十一所示,pcr缓冲液1-pcr缓冲液7的组分及含量如下表十二所示,甲状腺结节的样本dna具体为经病理分析后判定为良性甲状腺结节的穿刺样本,dna的含量为60ng,其被测对象为同一个患者,其电泳图如图5所示,电泳图中各基因片段的跑胶带的清晰度相对于实施例1至实施例3略差,但其电泳图与实施例1的基本一致,测得的基因序列也与实施例1相同。
表十一pcr反应体系
表十二pcr缓冲液1-pcr缓冲液7的组分及含量
综上,本发明的试剂盒能够同时检测多种基因变异,即便是甲状腺结节的样本量较少,依旧能够正常扩增出目的基因,同时使得检测变得简单、容易操作,能够为临床诊断甲状腺结节的良恶性以及判断预后提供辅助作用,有效降低了错判、误判的概率。
本具体实施例仅仅是对本发明的解释,其并不是对本发明的限制,本领域技术人员在阅读完本说明书后可以根据需要对本实施例做出没有创造性贡献的修改,但只要在本发明的权利要求范围内都受到专利法的保护。
序列表
<110>上海安甲生物科技有限公司
<120>鉴别人甲状腺结节良恶性的试剂盒及其使用方法和应用
<160>49
<170>siposequencelisting1.0
<210>1
<211>36
<212>dna
<213>人工序列(artificialsequence)
<400>1
tttggtctagctacagtgaaatctcgatggagtggg36
<210>2
<211>36
<212>dna
<213>人工序列(artificialsequence)
<400>2
tttggtctagctacagagaaatctcgatggagtggg36
<210>3
<211>36
<212>dna
<213>人工序列(artificialsequence)
<400>3
tttggtctagctacagtggaatctcgatggagtggg36
<210>4
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>4
gtggtagttggagctggtggcgtaggcaagagtgc35
<210>5
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>5
gtggtagttggagctagtggcgtaggcaagagtgc35
<210>6
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>6
gtggtagttggagcttgtggcgtaggcaagagtgc35
<210>7
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>7
gtggtagttggagctgatggcgtaggcaagagtgc35
<210>8
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>8
gtggtagttggagctgttggcgtaggcaagagtgc35
<210>9
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>9
gtggtagttggagctggtcgcgtaggcaagagtgc35
<210>10
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>10
gtggtagttggagctggttgcgtaggcaagagtgc35
<210>11
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>11
gtggtagttggagctggtgacgtaggcaagagtgc35
<210>12
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>12
ctggatacagctggacaagaagagtacagtgcc33
<210>13
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>13
ctggatacagctggaaaagaagagtacagtgcc33
<210>14
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>14
ctggatacagctggacgagaagagtacagtgcc33
<210>15
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>15
ctggatacagctggactagaagagtacagtgcc33
<210>16
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>16
ctggatacagctggacatgaagagtacagtgcc33
<210>17
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>17
ctggatacagctggacacgaagagtacagtgcc33
<210>18
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>18
gtggtggtgggcgccggcggtgtgggcaagagt33
<210>19
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>19
gtggtggtgggcgccgtcggtgtgggcaagagt33
<210>20
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>20
ctggataccgccggccaggaggagtacagcgcc33
<210>21
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>21
ctggataccgccggcaaggaggagtacagcgcc33
<210>22
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>22
ctggataccgccggccgggaggagtacagcgcc33
<210>23
<211>29
<212>dna
<213>人工序列(artificialsequence)
<400>23
cctcccgggtccccggcccagccccctcc29
<210>24
<211>29
<212>dna
<213>人工序列(artificialsequence)
<400>24
cctcccgggtccccggcccagccccttcc29
<210>25
<211>29
<212>dna
<213>人工序列(artificialsequence)
<400>25
ccttccgggtccccggcccagccccctcc29
<210>26
<211>28
<212>dna
<213>人工序列(artificialsequence)
<400>26
ttgctctgataggaaaatgagatctact28
<210>27
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>27
tcagtggaaaaatagcctcaattct25
<210>28
<211>30
<212>dna
<213>人工序列(artificialsequence)
<400>28
tactgttttcctttacttactacacctcag30
<210>29
<211>26
<212>dna
<213>人工序列(artificialsequence)
<400>29
ggaaaaatagcctcaattcttaccat26
<210>30
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>30
tggagtatttgatagtgtattaaccttatgtgt33
<210>31
<211>27
<212>dna
<213>人工序列(artificialsequence)
<400>31
tttacctctattgttggatcatattcg27
<210>32
<211>31
<212>dna
<213>人工序列(artificialsequence)
<400>32
accttatgtgtgacatgttctaatatagtca31
<210>33
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>33
ggatcatattcgtccacaaaatg23
<210>34
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>34
tccctgcccccttaccct18
<210>35
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>35
ggttaatatccgcaaatgacttgc24
<210>36
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>36
gcccccttaccctccaca18
<210>37
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>37
ccgcaaatgacttgctattattga24
<210>38
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>38
cacggaaggtcctgaggg18
<210>39
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>39
aagacttggtgttgttgatggc22
<210>40
<211>22
<212>dna
<213>人工序列(artificialsequence)
<400>40
cttggcaggtggggcaggagac22
<210>41
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>41
ctagaggaagcaggagacag20
<210>42
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>42
gaggagcgatgacggaatat20
<210>43
<211>16
<212>dna
<213>人工序列(artificialsequence)
<400>43
tgctggcacctggacg16
<210>44
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>44
tccctgagccctgtcctc18
<210>45
<211>21
<212>dna
<213>人工序列(artificialsequence)
<400>45
aaacacacacaggaagccctc21
<210>46
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>46
cgattcgacctctctccgct20
<210>47
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>47
gcgctgcctgaaactcgc18
<210>48
<211>20
<212>dna
<213>人工序列(artificialsequence)
<400>48
agtggattcgcgggcacaga20
<210>49
<211>18
<212>dna
<213>人工序列(artificialsequence)
<400>49
cagcgctgcctgaaactc18
- 还没有人留言评论。精彩留言会获得点赞!