甘蓝型油菜芥菜细胞质雄性不育育性恢复基因的分子标记的制作方法
本发明属于农作物分子育种技术领域,更具体地,涉及甘蓝型油菜芥菜细胞质雄性不育育性恢复基因的分子标记。
背景技术:
油菜是我国乃至世界最重要的油料作物之一,是人类重要的食用油来源。大量的事实和研究表明,利用杂种优势可以显著提高油菜产量。利用细胞质雄性不育(cms)生产杂交种是油菜杂种优势利用最为广泛的育种途径。
目前,全世界油菜生产上应用的细胞质雄性不育类型主要包括萝卜细胞质雄性不育(ogucms)、波里马细胞质雄性不育(polcms)和陕2a细胞质雄性不育等。其中ogucms由日本学者ogura于1968年在萝卜群体中发现,后由法国学者转育到甘蓝型油菜中。ogucms败育彻底,而且其育性不受温度和光照条件影响。在欧洲萝卜中发现的ogu恢复基因也被导入了甘蓝型油菜,实现了ogucms的三系配套,并用于油菜杂交种选育。波里马细胞质雄性不育系(polcms)是华中农业大学傅廷栋院士于1972年在欧洲引进的甘蓝型油菜品种波里马中发现的。1976年湖南省农业科学院首先实现了该系统的三系配套。目前,我国70%以上的油菜杂交种均由polcms选育而成。它可以分为低温不育型、高温不育型和稳定不育型三类,对温度的敏感性主要取决于细胞核,即保持系。鉴于我国油菜杂交种不育胞质类型较为单一,同时存在一定的制种风险,因此选育新型稳定的不育胞质类型对于油菜杂种优势利用具有重要意义。
wjs1acms是已经发现的一个来源于芥菜型油菜的不育胞质类型,该不育类型已导入甘蓝型油菜不育系wnj01a。通过多年不同生态环境(春油菜区和冬油菜区)下的育性鉴定,该不育系败育彻底,为无花粉类型,而且其育性不受温度和光照条件的影响。同时,研究学者将其与白菜品种上海青或北京大白菜杂交,在杂交后代中选育了稳定的恢复系hui(恢)01,该恢复系可以完全恢复wnj01a的育性。
然而现有技术还未报道甘蓝型油菜芥菜细胞质雄性不育系育性恢复基因的分子标记。
技术实现要素:
为了解决现有技术中不能高效地鉴定甘蓝型油菜芥菜细胞质雄性不育育性恢复基因的问题,本发明提供了indel分子标记可用于甘蓝型油菜芥菜细胞质雄性不育系恢复系的选育,该indel分子标记包括idc506、idc551、idc705、idc822、idc860、idc865中的一种或多种。
其中,idc506的引物对为:
如seqidno.1所示:tgttcgagaaccatggtcaa;
如seqidno.2所示:ttaccgaagagatcagcgct。
idc551的引物对为:
如seqidno.3所示:catgtaaccgcctctcttcc;
如seqidno.4所示:gattggaacgagaccaagga。
idc705的引物对为:
如seqidno.5所示:aaaatgcttgcgaaagagga;
如seqidno.6所示:atcttgagttatgggcgtgc。
idc822的引物对为:
如seqidno.7所示:tttgcttggcaacttctcac;
如seqidno.8所示:aactcccttcccagcttttc。
idc860的引物对为:
如seqidno.9所示:acccaagcctctgctagtga;
如seqidno.10所示:tcggttggttaaggtagaaagc。
idc865的引物对为:
如seqidno.11所示:ggccctaaaccatggagtct;
如seqidno.12所示:atgtgtaaagtgcagcgtgg。
使用上述分子标记中的一种或几种均可检测出待测材料是否具有恢复基因。
为了提高其检测准确率,该indel分子标记包括idc506、idc551、idc705、idc822、idc860、idc865中的两种或多种。进一步优选包括idc506、idc551、idc705、idc822、idc860和idc865。进一步优选地是,该indel分子标记为idc506、idc551、idc705、idc822、idc860和idc865。
在本发明中,甘蓝型油菜芥菜细胞质雄性不育系优选为wnj01a。其中,甘蓝型油菜芥菜细胞质雄性不育系恢复系优选为hui01。恢复基因优选为rfw。
进行pcr扩增后,当标记的idc506、idc551、idc705、idc822、idc860、idc865中具有恢复基因特异的目标条带时,则待测材料具有恢复基因的概率分别可达94.50%、98.39%、99.31%、98.85%、97.02%和96.65%。标记idc506和idc551位于rfw基因的一侧,idc705、idc822、idc860和idc865则位于该基因的另一侧。当两侧标记分别两两组合使用,同时具有恢复基因特异的目标条带时,则检测材料具有恢复基因的概率为100%。
其中,本发明实施方式中,扩增的pcr反应体系为:(10μl):1×taqbuffer,15mmmg+,2mmdntp,0.2utaqdna聚合酶(thermoscientific公司),正、反向引物各2μm,100ng模板dna,补充ddh2o至终体积10μl。
pcr程序如下:(1)94℃预变性3min,1个循环;(2)94℃变性30s,58℃复性30s,72℃延伸30s,35个循环;(3)72℃延伸5min,1个循环,运行结束后4℃保存备用。
在一个优选实施方式中,
标记idc506在恢复系hui01中扩增的核苷酸片段大小为222bp,具体核苷酸序列如下:
5'-tgttcgagaaccatggtcaatgtttaccacaatcaagacgagataaaaaaagtgtttttaccagggcgagaatgtatcacgcacctgcaaatgtgagcgctagaacgccagaaagtatcacggcctttgtcgctgtcaaaactgaaaaactcaagcgaacaatcagcttccagtggcctattcatgtcccagaggacatcgtttaccgaagagatcagcgct-3',如seqidno.13所示。
标记idc506在不育系wnj01a中扩增的核苷酸片段大小为203bp,具体核苷酸序列如下:
5'-tgttcgagaaccatggtcaatgtttaccacaatcaagacgagataaaaaaagtgtttttaccagggcgagaatgtgagcgctagaacgccagaaagtatcacggcctttgtcgctgtcaaaactgaaaaactcaagcgaacaatcagcttccagtggcctattcatgtcccagaggacatcgtttaccgaagagatcagcgct-3',如seqidno.14所示。
标记idc551在恢复系hui01中扩增的核苷酸片段大小为159bp,具体核苷酸序列如下:
5'-catgtaaccgcctctcttcccacactctccatagtaccctatttgaaagtaaccaaggagtccatttttgagacatagtaatgatcaaaggcttgtaaatggacttaagaaagaacttgttttcaaacctttggagatagattggaacgagaccaagga-3',如seqidno.15所示。
标记idc551在不育系wnj01a中扩增的核苷酸片段大小为156bp,具体核苷酸序列如下:
5'-catgtaaccgcctctcttcccacactttctcatagtaccctatcgtaagaaagaaaaggagtccagtcttgagacatagcaatgatcaaatgcttgtaaatggacttatcaaagaacttttcaacctttggagatggattggaacgagaccaagga-3',如seqidno.16所示。
标记idc705在恢复系hui01中扩增的核苷酸片段大小为198bp,具体核苷酸序列如下:
5'-aaaatgcttgcgaaagaggaggtaatattttttttttgctaataagaagttccgactactttgggttcgttatctcttttcatctttggaccaatctttataagtactacgtttaaaggcgtgaaacaagattcgagcttaagaacacaacgcaaccttccttttgatacattgagggatcttgagttatgggcgtgc-3',如seqidno.17所示。
标记idc705在不育系wnj01a中扩增核苷酸片段大小为183bp,具体核苷酸序列如下:
5'-aaaatgcttgcgaaagaggaggtgatattttctttttttttgctaataagaagttccgactactttgggtttggacctatctttataagtactacgtttaaaagcgtgaaacaagattcgagcttaagaacacaacgcaaccgtccttttgatacattgagggatcttgagttatgggcgtgc-3',如seqidno.18所示。
标记idc822在恢复系hui01中扩增的核苷酸片段大小为218bp,具体核苷酸序列如下:
5'-tttgcttggcaacttctcactagatgtgcttttcctcggtgcctagaaaccaagattgtacaagtgatattcagacaagatgtatgatgcaaaccagtttattcagaagagagcttactgctaaactcctagcatcaggggttgaatcacgtttggtaagcttcttcagccctgagctatctgaagctctgatatctaaactcccttcccagcttttc-3',如seqidno.19所示。
标记idc822在不育系wnj01a中扩增的核苷酸片段大小为223bp,具体核苷酸序列如下:
5'-tttgcttggcaacttctcactagatgtgcttttccgcggcgcctagaaaccaagattgtagaaggtatattaaccctttgttagtatcaaagccaaaggaagctaaagaagaagagagcttactattaaactcctggcatcaggggttgaatcacgtttggtaagcttcttcagccctgagctatctgaagctctgatatctaaactcccttcccagcttttc-3',如seqidno.20所示。
标记idc860在恢复系hui01中扩增的核苷酸片段大小为186bp,具体核苷酸序列如下:
5'-acccaagcctctgctagtgagcaacaatagttactatttatttacacaattgcttcaatttttccttgatattgttttcattaactcaaacttcctttgtacgttggaaaaaaaaagtattttttgttattatttgaggatattcatttaaaattatatttttgtcggttggttaaggtagaaagc-3',如seqidno.21所示。
标记idc860在不育系wnj01a中扩增的核苷酸片段大小为147bp,具体核苷酸序列如下:
5'-acccaagcctctgctagtgagcaacaatagttactatttatttacacaattgcttcaatttttccttgataaaaaaagtattttttgttattatttgaggatattcatttaaaattatatttttgtcggttggttaaggtagaaagc-3',如seqidno.22所示。
标记idc865在恢复系hui01中扩增的核苷酸片段大小为207bp,具体核苷酸序列如下:
5'-ggccctaaaccatggagtctccacttttttttcaagatttttttttaatggattttttcttggtgtggtttttaatgaaagaggtcttcatggtttycaaactaaaccatgtttgatcggtttccttgatcaagcttgagggggagtgttgagatgagagggtacttgttgagagaaatgcagtgaaatgtgtaaagtgcagcgtgg-3',如seqidno.23所示。
标记idc865在不育系wnj01a中扩增的核苷酸片段大小为219bp,具体核苷酸序列如下:
5'-ggccctaaaccatggagtctccactcttttttcaagatttttttttaatggattttttcctgatgtggtttttaatgaaagaggtcttcatggtttccaaactaaaccatgtttgatcggtttccttgatcaagcttgagggggagtgttgagaggagtgttgagatgagagggtacttgttgagagaaatgcagtgaaatgtgtaaagtgcagcgtgg-3',如seqidno.24所示。
本发明的另一个方面,还提供了上述indel分子标记在辅助选育优良恢复系中的应用。
在本发明一个优选实施方式中,上述应用中恢复系优选为hui01。
在本发明一个优选实施方式中,上述indel分子标记包括idc506、idc551、idc705、idc822、idc860和idc865。
当检测待选育或待筛选的材料时,当其pcr扩增后的核苷酸序列若出现idc506、idc551、idc705、idc822、idc860和idc865任一分子标记在恢复系如hui01中扩增的核苷酸序列时,即可在误差范围内说明该材料为恢复系如hui01。
其中,idc506在恢复系hui01中扩增的核苷酸序列如seqidno.13所示;idc551在恢复系hui01中扩增的核苷酸序列如seqidno.15所示;idc705在恢复系hui01中扩增的核苷酸序列如seqidno.17所示;idc822在恢复系hui01中扩增的核苷酸序列如seqidno.19所示;idc860在恢复系hui01中扩增的核苷酸序列如seqidno.21所示;idc865在恢复系hui01中扩增的核苷酸序列如seqidno.23所示。
本发明提供的indel分子标记可以有效地鉴定甘蓝型油菜芥菜细胞质雄性不育系恢复系,可用于该基因的图位克隆和分子标记辅助选择,加快新优良恢复系的选育。
附图说明
图1为本发明实施例1中indel标记idc506、idc551、idc705、idc822、idc860和idc865在f2群体单株的验证和应用的结果图;f:可育单株;s:不可育单株;a:不育系wnj01a;b:恢复系hui01;其中,箭头指示分子标记的多态性条带;
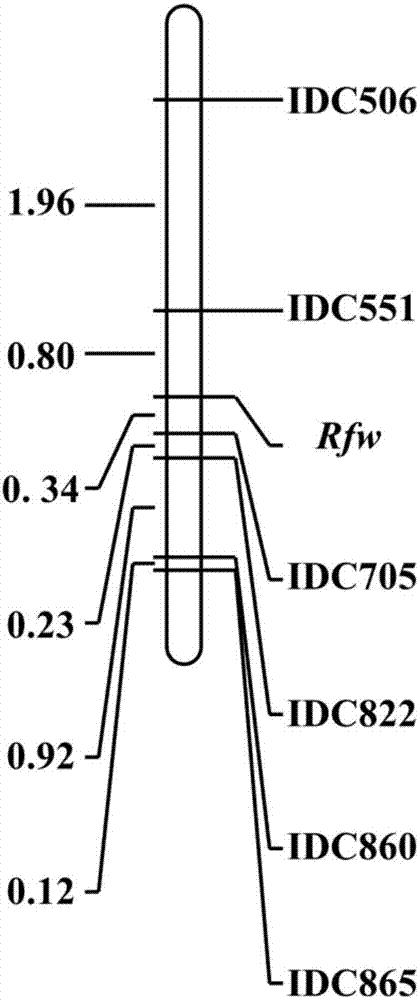
图2为本发明实施例3中甘蓝型油菜a09染色体标记rfw基因位置图;其中,左边数字指示分子标记间的遗传距离。
具体实施方式
下面结合实施例,对本发明的具体实施方式作进一步详细描述。以下实施例用于说明本发明,但不用来限制本发明的范围。
若未特别指明,实施例中所用的技术手段为本领域技术人员所熟知的常规技术手段。若未特别指明,实施例中所用的试剂为市售。
实施例1:构建定位群体及恢复基因的遗传分析
以不育系wnj01a为母本与恢复系hui01为父本杂交,f1杂种表现为完全可育,表明育性恢复性状受显性基因控制。自交获得的f2群体共包括2161个单株,田间调查显示可育单株数目为1606,不育单株为555。卡平方测验(χ2test)结果显示,可育与不育单株分离比例符合3:1(χ2=0.50<χ20.05,1=3.84,p>0.05),表明育性的恢复受单个显性基因位点控制,该基因被命名为rfw。
实施例2:恢复基因rfw分子标记的开发
利用ctab法(李佳等,1994)提取植株总dna,在f2群体中选取极端可育单株37株和极端不育单株38株,以每个单株80ngdna等量混合,分别构建可育混合池(f-bulk)和不育混合池(s-bulk)。利用第二代测序技术(ngs)对混合池进行测序(bsa-seq)结合qtl-seq方法进行分析,将rfw基因定位在甘蓝型油菜a09染色体的候选区间(chr.a09:27.62-33.87mb,大小为6.25mb)内。在该区间内我们共开发indel标记203个,在亲本、dna混合池中进行初步分析,并在部分极端不育单株和极端可育单株中进行进一步分析。
标记扩增的pcr反应体系(10μl):1×taqbuffer,15mmmg+,2mmdntp,0.2utaqdna聚合酶(thermoscientific公司),正、反向引物各2μm,100ng模板dna,补充ddh2o至终体积10μl。
pcr程序如下:(1)94℃预变性3min,1个循环;(2)94℃变性30s,58℃复性30s,72℃延伸30s,35个循环;(3)72℃延伸5min,1个循环,运行结束后4℃保存备用。
电泳:在pcr扩增产物中加入10μl上样缓冲液(98%去离子甲酰胺、10mmedta、0.005%二甲苯青ff和0.005%溴酚蓝),95℃变性5min后,冰浴中冷却,4℃放置备用。利用6%聚丙烯酰胺凝胶电泳分离pcr产物,银染、显影后,获得每个单株标记基因型的数据。
结果显示,共开发多态性条带清晰且与rfw连锁较近的分子标记共6个,分别为idc506、idc551、idc705、idc822、idc860和idc865。
实施例3、恢复基因rfw分子标记的应用
将标记idc506、idc551、idc705、idc822、idc860和idc865在上述f2群体中进行验证和应用,方法同实施例2(图1)。结果显示,idc506和idc551位于恢复基因rfw的一侧,遗传距离分别为2.76和0.80cm;idc705、idc822、idc860和idc865位于另一侧,遗传距离分别为0.34、0.57、1.49和1.61cm(图2)。idc551和idc705区间位于甘蓝型油菜a9染色体30.9-32.0mb的物理位置,大小为1.1mb。当标记idc506、idc551、idc705、idc822、idc860和idc865具有恢复基因特异的目标条带时,则检测材料具有恢复基因的概率分别为94.50%、98.39%、99.31%、98.85%、97.02%和96.56%。当两侧标记分别两两组合同时具有恢复基因特异的目标条带时,则检测材料具有恢复基因的概率为100%。以上研究结果显示,上述分子标记可用于rfw基因的分子标记辅助选择。
最后,本发明的方法仅为较佳的实施方案,并非用于限定本发明的保护范围。凡在本发明的精神和原则之内,所作的任何修改、等同替换、改进等,均应包含在本发明的保护范围之内。
序列表
<110>华中农业大学
<120>甘蓝型油菜芥菜细胞质雄性不育育性恢复基因的分子标记
<130>khp171115371.7
<160>24
<170>siposequencelisting1.0
<210>1
<211>20
<212>dna
<213>idc506
<400>1
tgttcgagaaccatggtcaa20
<210>2
<211>20
<212>dna
<213>idc506
<400>2
ttaccgaagagatcagcgct20
<210>3
<211>20
<212>dna
<213>idc551
<400>3
catgtaaccgcctctcttcc20
<210>4
<211>20
<212>dna
<213>idc551
<400>4
gattggaacgagaccaagga20
<210>5
<211>20
<212>dna
<213>idc705
<400>5
aaaatgcttgcgaaagagga20
<210>6
<211>20
<212>dna
<213>idc705
<400>6
atcttgagttatgggcgtgc20
<210>7
<211>20
<212>dna
<213>idc822
<400>7
tttgcttggcaacttctcac20
<210>8
<211>20
<212>dna
<213>idc822
<400>8
aactcccttcccagcttttc20
<210>9
<211>20
<212>dna
<213>idc860
<400>9
acccaagcctctgctagtga20
<210>10
<211>22
<212>dna
<213>idc860
<400>10
tcggttggttaaggtagaaagc22
<210>11
<211>20
<212>dna
<213>idc865
<400>11
ggccctaaaccatggagtct20
<210>12
<211>20
<212>dna
<213>idc865
<400>12
atgtgtaaagtgcagcgtgg20
<210>13
<211>222
<212>dna
<213>idc506-pcr
<400>13
tgttcgagaaccatggtcaatgtttaccacaatcaagacgagataaaaaaagtgttttta60
ccagggcgagaatgtatcacgcacctgcaaatgtgagcgctagaacgccagaaagtatca120
cggcctttgtcgctgtcaaaactgaaaaactcaagcgaacaatcagcttccagtggccta180
ttcatgtcccagaggacatcgtttaccgaagagatcagcgct222
<210>14
<211>203
<212>dna
<213>idc506-pcr
<400>14
tgttcgagaaccatggtcaatgtttaccacaatcaagacgagataaaaaaagtgttttta60
ccagggcgagaatgtgagcgctagaacgccagaaagtatcacggcctttgtcgctgtcaa120
aactgaaaaactcaagcgaacaatcagcttccagtggcctattcatgtcccagaggacat180
cgtttaccgaagagatcagcgct203
<210>15
<211>159
<212>dna
<213>idc551-pcr
<400>15
catgtaaccgcctctcttcccacactctccatagtaccctatttgaaagtaaccaaggag60
tccatttttgagacatagtaatgatcaaaggcttgtaaatggacttaagaaagaacttgt120
tttcaaacctttggagatagattggaacgagaccaagga159
<210>16
<211>156
<212>dna
<213>idc551-pcr
<400>16
catgtaaccgcctctcttcccacactttctcatagtaccctatcgtaagaaagaaaagga60
gtccagtcttgagacatagcaatgatcaaatgcttgtaaatggacttatcaaagaacttt120
tcaacctttggagatggattggaacgagaccaagga156
<210>17
<211>198
<212>dna
<213>idc705-pcr
<400>17
aaaatgcttgcgaaagaggaggtaatattttttttttgctaataagaagttccgactact60
ttgggttcgttatctcttttcatctttggaccaatctttataagtactacgtttaaaggc120
gtgaaacaagattcgagcttaagaacacaacgcaaccttccttttgatacattgagggat180
cttgagttatgggcgtgc198
<210>18
<211>183
<212>dna
<213>idc705-pcr
<400>18
aaaatgcttgcgaaagaggaggtgatattttctttttttttgctaataagaagttccgac60
tactttgggtttggacctatctttataagtactacgtttaaaagcgtgaaacaagattcg120
agcttaagaacacaacgcaaccgtccttttgatacattgagggatcttgagttatgggcg180
tgc183
<210>19
<211>218
<212>dna
<213>idc822-pcr
<400>19
tttgcttggcaacttctcactagatgtgcttttcctcggtgcctagaaaccaagattgta60
caagtgatattcagacaagatgtatgatgcaaaccagtttattcagaagagagcttactg120
ctaaactcctagcatcaggggttgaatcacgtttggtaagcttcttcagccctgagctat180
ctgaagctctgatatctaaactcccttcccagcttttc218
<210>20
<211>223
<212>dna
<213>idc822-pcr
<400>20
tttgcttggcaacttctcactagatgtgcttttccgcggcgcctagaaaccaagattgta60
gaaggtatattaaccctttgttagtatcaaagccaaaggaagctaaagaagaagagagct120
tactattaaactcctggcatcaggggttgaatcacgtttggtaagcttcttcagccctga180
gctatctgaagctctgatatctaaactcccttcccagcttttc223
<210>21
<211>186
<212>dna
<213>idc860-pcr
<400>21
acccaagcctctgctagtgagcaacaatagttactatttatttacacaattgcttcaatt60
tttccttgatattgttttcattaactcaaacttcctttgtacgttggaaaaaaaaagtat120
tttttgttattatttgaggatattcatttaaaattatatttttgtcggttggttaaggta180
gaaagc186
<210>22
<211>147
<212>dna
<213>idc860-pcr
<400>22
acccaagcctctgctagtgagcaacaatagttactatttatttacacaattgcttcaatt60
tttccttgataaaaaaagtattttttgttattatttgaggatattcatttaaaattatat120
ttttgtcggttggttaaggtagaaagc147
<210>23
<211>207
<212>dna
<213>idc865-pcr
<400>23
ggccctaaaccatggagtctccacttttttttcaagatttttttttaatggattttttct60
tggtgtggtttttaatgaaagaggtcttcatggtttycaaactaaaccatgtttgatcgg120
tttccttgatcaagcttgagggggagtgttgagatgagagggtacttgttgagagaaatg180
cagtgaaatgtgtaaagtgcagcgtgg207
<210>24
<211>219
<212>dna
<213>idc865-pcr
<400>24
ggccctaaaccatggagtctccactcttttttcaagatttttttttaatggattttttcc60
tgatgtggtttttaatgaaagaggtcttcatggtttccaaactaaaccatgtttgatcgg120
tttccttgatcaagcttgagggggagtgttgagaggagtgttgagatgagagggtacttg180
ttgagagaaatgcagtgaaatgtgtaaagtgcagcgtgg219
- 还没有人留言评论。精彩留言会获得点赞!