先将片段进行融合然后转化构成载体的构建方法与流程
本发明涉及基因工程遗传育种学和生物遗传改良技术领域,特别涉及一种先将片段进行融合然后转化构成载体的构建方法。
背景技术:
水稻作为世界上超过一半人口的主食,是最重要的粮食作物之一.在过去的半个多世纪里,水稻育种取得了巨大的成功。
水稻的单位产量实现了倍增,部分地方甚至提高至3倍,这为保障世界粮食安全作出了巨大的贡献.但近十几年来水稻的产量停滞不前,这一方面是由于在育种技术上没有新的突破以及遗传多样性在栽培品种中的逐步变窄,另一方面也是因为频繁发生的病虫害以及旱灾等自然灾害使得水稻生产损失惨重。
然而,世界人口的持续增长以及社会经济的快速发展导致对粮食的需求不断增加。针对这些问题,我国学者提出了培育绿色超级稻的设想,围绕水稻抗病虫、抗旱、营养高效利用、优质、高产等五大重要性状,对水稻品种进行全面改良以实现农业的可持续发展。而转基因技术作为一种新兴的育种手段,在实现绿色超级稻目标上将发挥重要作用.
水稻的转基因研究始于20世纪80年代末期,迄今已有大量的转基因水稻研究被报道。
水稻转基因技术始于原生质体培养,1985年首次成功地从水稻原生质体再生完整植株;1988年在粳稻品种中获得第一批转基因水稻植株;1990年从籼稻品种chinsurahboroii中获得第一例转基因籼稻植株;1990年李宝健等用农杆菌感染水稻组织获得转化愈伤组织;1991年利用水稻幼胚作为受体材料,用基因枪法,成功获得转基因植株,并且转化效率明显提高。
从此,幼胚作为转基因受体材料得到广泛研究应用。1993年用农杆菌法在粳稻品种上获得了转基因植株,此后,基因枪轰击法和农杆菌介导法作为最有价值的转化途径广泛用于水稻转基因研究。
根据第三代不育系的原理,我们最终拿到的不育系不含有任何转基因元件,而得到的保持系则仅含有:筛选标记基因-花粉致死基因-育性恢复基因三个基因,其中筛选标记基因是红色荧光蛋白(dsred),来自礁珊瑚(discosomasp.),利用种子特异表达的启动子使dsred基因在种子种特异表达来筛选不育系的种子;花粉致死基因是玉米α淀粉酶基因(zmaa1),来自玉米,可使携带该基因的花粉粒败育;育性恢复基因在水稻中一般是普通隐性核不育基因,来自水稻本身,可使相应基因突变体株系恢复育性。
技术实现要素:
本发明所要解决的技术问题在于,提供了一种先将片段进行融合然后转化构成载体的构建方法。本发方法将潮霉素抗性基因与红色荧光基因(dsred)基因进行连锁后转化水稻成熟胚诱导的愈伤组织,在愈伤组织细胞培养筛选阶段加入潮霉素,同时结合红色荧光检测,快速、有效的筛选。
为解决上述技术问题,本发明提供了一种先将片段进行融合然后转化构成载体的构建方法,包括以下步骤:
a、提取待转化作物dna;
b、分别获得多种连锁基因表达盒;
c、获取去除hpt基因的pcambia1300质粒的;
d、各个表达盒的连接;
e、融合片段与pcambia1300-hpt-质粒的连接。
所述先将片段进行融合然后转化构成载体的构建方法,进一步包括:构建双t-dna载体,其中一个t-dna区含有三连锁基因,另一个t-dna区含有抗性基因,用于愈伤转化及植株再生阶段的筛选;所述三连锁基因分别为:dsred基因、eat1基因、zmaa基因。
构建含有eat1基因的t-dna区的方法包括:以步骤a获得的dna为模板,以eat1-f:cgatcgtcctatta
构建含有dsred基因的t-dna区的方法包括:以含有dsred片段的pgdr质粒为模板,利用dsred-f:gagatccactagttctagag
构建含有zmaa基因的t-dna区的方法包括:以玉米dna为模板,以zmaa-f:gacctgcaggcatgcaagct
为解决上述技术问题,本发明还提供了一种在构建含有eat1基因的t-dna区的载体中使用的引物,引物序列为:eat1-f:cgatcgtcctatta
为解决上述技术问题,本发明又提供了一种在构建含有dsred基因的t-dna区的载体中使用的引物,引物序列为:dsred-f:gagatccactagttctagag
为解决上述技术问题,本发明另提供了一种在构建含有zmaa基因的t-dna区的载体中使用的引物,引物序列为:zmaa-f:gacctgcaggcatgcaagct
为解决上述技术问题,本发明再提供了一种如权利要求前述任一项引物在载体构建和或工程菌株构建中的应用。
为解决上述技术问题,本发明还提供了一种如前述任一项所述构建方法构建的载体。
本发明有益效果包括:本发明先将片段进行融合然后转化构成载体的构建方法,构建了双t-dna载体,其中一个t-dna区含有上述的三连锁基因,另一个t-dna区含有潮霉素或者卡那霉素等抗性基因,用于愈伤转化及植株再生阶段的筛选。
附图说明
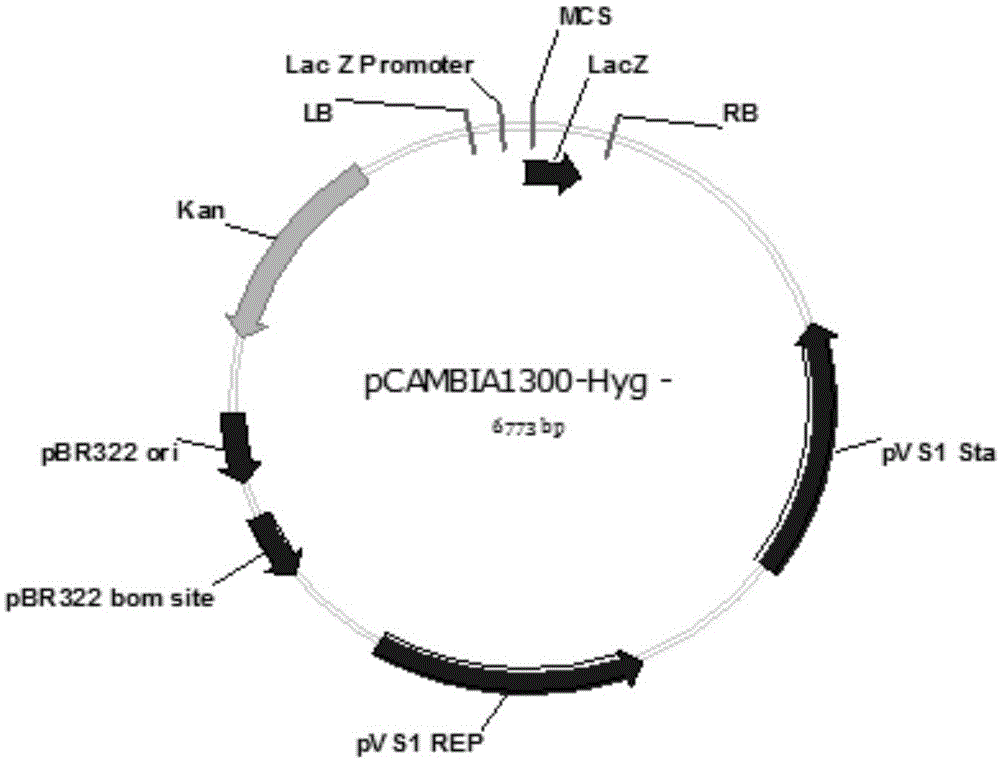
图1为本发明实施例所述去除hyg抗性基因后的pcambia1300质粒图谱;
图2为本发明实施例所述dsred表达盒电泳检测图;
图3为本发明实施例所述eat1表达盒电泳检测图;
图4为本发明实施例所述zmaa1表达盒电泳检测。
具体实施方式
下面结合实施例详述本发明。为使本发明的目的、技术方案及优点更加清楚、明确,以下对本发明进一步详细说明,但本发明并不局限于这些实施例。
本发明将潮霉素抗性基因与红色荧光基因(dsred)基因进行连锁后转化水稻成熟胚诱导的愈伤组织,在愈伤组织细胞培养筛选阶段加入潮霉素,同时结合红色荧光检测,快速、有效的的筛选。
在本发明一实施例中,提供了一种先将片段进行融合然后转化构成载体的构建方法,包括以下步骤:
a、提取待转化作物dna;
b、分别获得多种连锁基因表达盒;
c、获取去除hpt基因的pcambia1300质粒的;
d、各个表达盒的连接;
e、融合片段与pcambia1300-hpt-质粒的连接。
所述先将片段进行融合然后转化构成载体的构建方法,进一步包括:构建双t-dna载体,其中一个t-dna区含有三连锁基因,另一个t-dna区含有抗性基因,用于愈伤转化及植株再生阶段的筛选;所述三连锁基因分别为:dsred基因、eat1基因、zmaa基因。
构建含有eat1基因的t-dna区的方法包括:以步骤a获得的dna为模板,以eat1-f:cgatcgtcctatta
构建含有dsred基因的t-dna区的方法包括:以含有dsred片段的pgdr质粒为模板,利用dsred-f:gagatccactagttctagag
构建含有zmaa基因的t-dna区的方法包括:以玉米dna为模板,以zmaa-f:gacctgcaggcatgcaagct
在本发明另一实施例中,提供了一种在构建含有eat1基因的t-dna区的载体中使用的引物,引物序列为:eat1-f:cgatcgtcctatta
在本发明又一实施例中,提供了一种在构建含有dsred基因的t-dna区的载体中使用的引物,引物序列为:dsred-f:gagatccactagttctagag
在本发明另一实施例中,提供了一种在构建含有zmaa基因的t-dna区的载体中使用的引物,引物序列为:zmaa-f:gacctgcaggcatgcaagct
在本发明另一实施例中,提供了一种如权利要求前述任一项引物在载体构建和或工程菌株构建中的应用。
在本发明另一实施例中,提供了一种如前述任一项所述构建方法构建的载体。
在本发明另一实施例中,采用以下技术方案予以实现:
a、dsred基因表达盒的获得;
b、eat1基因表达盒的获得
c、zmaa基因表达和盒的获得
d、双t载体的改造
e、各表达盒的连接
实验步骤:
1、用ctab法提取水稻的dna,具体操作如下:
1.1.用液氮研磨1g左右植物组织,将研磨后的粉末转移到预冷的离心管中;
1.2.向离心管中加入500μl2×ctab(已预热至65℃),颠倒混匀后在65℃水浴中放置30~60min,期间要上下颠倒混匀数次;
1.3.取出离心管,加入等体积的24∶1(三氯甲烷∶异戊醇),上下颠倒混匀;
1.4.12000rpm,离心10min,取出后将上层水相转移至一新的离心管中;
1.5.向离心管中加入2倍体积预冷的无水乙醇,-20℃沉淀15min至过夜;
1.6.12000rpm离心10min,去上清,然后加入700μl70%的乙醇,上下颠倒数次,洗涤沉淀;12000rpm离心5min,去上清,重复该过程1次;
1.7.12000rpm离心10min,去上清,倒置于吸水纸上数分钟,最后置于超净台中吹干;
1.8.在离心管中加入30~50μl的灭菌去离子水或者te溶液,4℃放置数小时使其充分溶解。
2、各表达盒的获得
(1)以1中的dna为模板,以eat1-f:cgatcgtcctatta
eat1-r:gtttaaacacaat
pcr扩增程序:94℃预变性5min;94℃,变性1min;56℃(视不同引物对而定),退火1min;72℃,延伸1min(视片段长度而定,1kb/min),30~35cycle;72℃,延伸10min;4℃保存。
(2)以含有dsred片段的pgdr质粒为模板,利用dsred-f:gagatccactagttctagag
扩增程序:
(3)以玉米dna为模板,以zmaa-f:gacctgcaggcatgcaagct
3、去除hpt基因的pcambia1300质粒的获取。
首先用asci将pcambia1300质粒酶切后自连环化,得到去除hpt基因的质粒pcambia1300-hpt-,具体的酶切体系和酶切程序如下:
然后在体系中加入t4连接酶2μl和10xt4buffer3μl,双蒸水定容到30μl,16℃下保持12hour,获得pcambia1300-hpt-环状质粒
4、各表达盒的连接
1.eat1表达盒、dsred表达盒和zmaa1表达盒三个片段的模板以1∶1∶1的个数比加入,使用koddna聚合酶,在不添加引物的情况下空循环5次;然后利用dsred-f-ecorif和eat1-r-hindiii引物进行扩增循环35次,具体反应体系如下:
2.pcr反应程序如下:
5、融合片段与pcambia1300-hpt-质粒的连接
首先对pcambia1300-hpt-环化的质粒双酶切,酶切体系如下:
将步骤4中的连接产物连接到处理后的载体上,连接体系
6、将上述反应液取10μl导入到农杆菌中,形成可以用于介导转化植物细胞的工程菌农杆菌菌株eha105。
农杆菌感受态细胞的制备
取-70℃保存的农杆菌于含50μg/ml利福平平板划线,28℃培养。
挑取单菌落接种于5mlym液体培养基中,220rpm28℃振荡培养12-16hr。
取2ml菌液转接于100mlym液体培养基中,28℃220rpm振荡培养至od600=0.5。
转入无菌离心管,5000rpm离心5min,去上清液。
加入10ml预冷的0.1m的cacl2溶液,轻轻悬浮细胞,冰上放置20min。4℃5000rpm离心5min,去上清。
加入4ml预冷的含15%甘油的0.1m的cacl2溶液,轻轻悬浮。
农杆菌悬浮液分装于无菌eppendorf管中,每管200μl冻存于-70℃。
转化农杆菌
取1μg左右的上述构建好的质粒dna加入到200ml农杆菌感受态细胞中,混匀后,冰浴30min,-70℃放置10min。再在37℃水浴5min或42℃水浴1min,接着冰浴2min,加入800mlym液体培养基28℃,175rpm摇培3hr后涂在含50μg/mlkanamycin的ym平板上。28℃培养到形成单菌落,
本发明提供了一种基于dsred荧光蛋白基因为报告基因的不含潮霉素抗性基因的工程菌株。
本发明还提供了一种将片段进行融合,然后转化载体的一种实验新思路。
其它说明
1、各表达盒扩增所需引物
dsred-f:gagatccactagttctagag
dsred-r:tgtgttttgcgaatgcggcc
dsred-f-ecoriggaattcgagatccactagttctagag
zmaa-f:gacctgcaggcatgcaagct
zmaa-r:tctttcccctatatctccacg
eat1-f:cgatcgtcctatta
eat1-r:gtttaaacacaat
eat1-r-hindiiicggatccgtttaaacacaat
以上所述,仅是本发明的几个实施例,并非对本发明做任何形式的限制,虽然本发明以较佳实施例揭示如上,然而并非用以限制本发明,任何熟悉本专业的技术人员,在不脱离本发明技术方案的范围内,利用上述揭示的技术内容做出些许的变动或修饰均等同于等效实施案例,均属于本发明技术方案保护范围内。
序列表
<110>青岛袁策集团有限公司
<120>先将片段进行融合然后转化构成载体的构建方法
<160>3
<170>siposequencelisting1.0
<210>1
<211>1875
<212>dna
<213>oryza.satival.
<400>1
tttgacctttattatatggtcataaagacccttcagcaaaatgattgttactgctatcgg60
cattttctgttgtttttcttttggaatcaatcttgtgtgacaccattgtattgtttcatg120
tcttgccactataatagtcttggcatagcactggatctcatgagtctttgagccgcaaat180
tcatgaacataagttctttccattcaaccgttggctgaggcaaagatacagatttggagc240
gaaggtgcctagcactgttttgccaaaatgattgttggggctggttactttgaggattcc300
cacgatcaaagtctcatggcaggatctttgatccatgactcaaatcaagctcctgcaagc360
agtgaaaacacaagcattgatttgcagaaattcaaagtgcacccgtactcaacagaagct420
ctctcgaatacggccaatctagctgaagctgcaagagcaattaaccaccttcaacatcaa480
ctagaaattgatttggagcaagaggttcccccagtagaaactgcaaactgggatccagct540
atctgcactataccagatcatatcatcaaccatcagtttagcgaagatccacaaaacata600
ttggtggagcaacagatccagcagtatgattctgcactttatccaaatggtgtttacaca660
cctgcaccagatctccttaatcttatgcagtgcacaatggctccagcattcccggcaacg720
acatccgtattcggtgacacaacactgaatggtactaactatttggatcttaacggtgaa780
cttacaggagtagcagcggttccagacagtgggagtgggttgatgtttgctagtgattca840
gctctccagttagggtaccatggtactcaatctcatctaataaaggatatctgccactcg900
ttgccccaaaattatgggctgtttcccagtgaggacgaacgagatgtgattattggtgtt960
ggaagtggagatctttttcaggagatagatgacaggcagtttgatagtgtacttgaatgc1020
aggagagggaagggtgagttcggaaagggcaagggaaaagctaattttgcaactgagaga1080
gagaggcgggagcagctaaatgtgaagttcaggaccctaagaatgctcttcccaaatcct1140
accaagaatgacagggcctcaatagtaggtgatgccattgagtatatagatgagctcaat1200
cgaacagtgaaggagctgaagatcctggtggaacagaagaggcatggaaataacaggaga1260
aaggtgttaaagttggatcaagaggcagccgctgatggcgagagctcatcgatgaggcca1320
gtgagggatgatcaagacaatcagctccatggagccataaggagctcatgggttcagagg1380
aggtcaaaggaatgccacgttgatgtccgcatactggacgatgaagtaaacatcaagctc1440
actgaaaagaagaaggccaactctctgcttcatgcagcaaaggttctagatgagttccag1500
ctcgagcttatccatgtagtgggtgggattataggtgatcaccatatattcatgttcaac1560
actaaggtatcagaaggttcggcggtttatgcatgtgcagtggcaaagaagctccttcaa1620
gcagtggacgtgcaacaccaggccctcgacatattcaactaatctttagcaacagtactg1680
attatctgaacaatgtcctagattttcagttaccttgctgagcaaacttatttgaccagg1740
attggagagaattttatctttagcactagctacctagcaaaacttcttaacaatttggcc1800
atgtaacggcttgctgctgtccggttgtacaccttaactagcctgactaggaaagctttg1860
atgcttgtcttgtgt1875
<210>2
<211>1549
<212>dna
<213>zeamaysl.
<400>2
ctctgagataagtgaagcatctcgcgcactgtcgcagtcgcagacggagatgatgaagca60
ctcgagcagcttgtgcttgctcttcctcttggcgctctgcaccaccctgctggcctgcgg120
cctggtccaggcacaagtcctcttccaggggtttaactgggagtcgtgcaagcagcaggg180
aggctggtacaacaggctcaaggcccaggtcgacgacatcgccaaggccggcgtcacgca240
cgtctggctgcctccaccctcgcactccgtctcgccacaaggctacatgccaggccgcct300
atacgacctggacgcgtccaagtacggcacggcggcggagctcaagtccctgatagcggc360
gttccacggcaggggcgtgcagtgcgtggcggacatcgtcatcaaccaccggtgcgcgga420
aaagaaggacgcgcgcggcgtgtactgcatcttcgagggcgggactcccgacgaccgcct480
ggactggggccccgggatgatctgcagcgacgacacgcagtactcggacgggacggggca540
ccgcgacacgggcgaggggttcgcggcggcgcccgacatcgaccacctcaacccgcgcgt600
gcagcgggagctctccgcctggctcaactggctcaggtccgacgccgtggggttcgacgg660
ctggcgcctcgacttcgccaagggctactcgccggccgtcgccagaatgtacgtggagag720
cacggggccgccgagcttcgtcgtcgcggagatatggaactcgctgagctacagcgggga780
cggcaagccggcgcccaaccaggaccagtgccggcaggagctgctggactggacgcgggc840
cgtcggcgggcccgccatggcgttcgacttccccaccaagggcctgctgcaggcgggcgt900
gcagggggagctgtggcggctgcgcgacagctccggcaacgcggccggcctgatcgggtg960
ggcgcccgagaaggccgtcaccttcgtcgacaaccatgacaccgggtcgacgcagaagct1020
ctggccgttcccatccgacaaggtcatgcagggctacgcctacatcctcacccatccagg1080
agtcccctgcattttctacgaccacatgttcgactggaacctgaagcaggagatatccac1140
gctgtctgccatcagggcgcggaacggcatccgcgccgggagcaagctgcggatcctcgt1200
ggcggacgcggacgcgtacgtggccgtcgtcgacgagaaggtcatggtgaagatcgggac1260
aaggtacggcgtgagcagcgtggtcccgtcggatttccacccggcggcgcacggcaagga1320
ctactgcgtctgggagaaagcgagcctccgcgtcccggcggggcgccacctctagcagct1380
cagattgctcagtcttgtgctgcattgcaaacacagcagcacgacactgcataacgtctt1440
ttccttaatttcctgaattttaccttttcctagttcaatttcatatatgtatttctacat1500
gtacacactatcacaatcagataaataaacaagcttggtcacctgaaag1549
<210>3
<211>2802
<212>dna
<213>zeamaysl.
<400>3
ttataagacggagctcattgtcgctcgtcagcgggttgatgctgaaacttcctattgtgg60
gtttgtatgcctcctcccgtccgacctgagcgttaaaatctccgataactatctgcacat120
gggcagcagatgtgctccatctccaactgcgtatagaagatctccgtctcgtcatcggag180
tttccaaggtgcggactgtacacattaataatgctgaggttgaagaacctgccacggatt240
cttagcctgcacattcgctcattgatcgatcaccatccgatcacccactttcgcatctcc300
cctatgatcaggaacaccgaaccgagctcatgcttttcaacccctgctctggtagattat360
gcagtcactgcgatggaggcgctccgaaacccctttccagcgcaactcttgtagtgctac420
tatttcgaagccgtcctcgtccataagaatgcgggtgctttcaggtgccgtgagtgatct480
gcagttccatgtctcgagtttccaatcgtgtgttttgtttcgcagcattggtctataatc540
gttgaatccgattcgaaacttcatggttttcgatcgttgcgtttatattgagggaggctt600
gcaaggctgcttccccgacacctcatctcgtcggagggacccgtaggacaggagggacga660
ccagccgcccctaacaaggagaacagaggctagctatccccctccactcaatttagccat720
atcacccatcttcccaagggattgggttttcacgtttacccaagctcagatatttggaga780
gacatgttaccattctatacgccgggaacgtattgaattgaagtgaggtggagagtctat840
gttaatcttcaagaggcttcggatccatactatatacaatatgagagatggttttcataa900
tattgggaaaaattcatctgagcatctccatctcaaacgcagcttaggaaggacaaagct960
aagatgtctcaaagacgtatttgaagtactggggactatacatgtctgtcagtccagcat1020
cgtccgcggcggacaagtattttgaagtggagaactttctcatgaccagttgacagccag1080
cacaactcaacatcaatgttggtgtcggacttgatttttgatccctgataagtgagtttt1140
gaacgatttcaaagatacgatcacctcgcccaagttggtggttttcggcccctttaactt1200
caacccgaggctaagtgccgatcgctcgatcctttggaaagctaggatagaagagcctca1260
aaccaatgatgtctatgtcatctatgtttggtgcggatacaccgccagtgaaacaagtgt1320
aataagaataaactttgattatttaatatttttttaccttcgcataatgtatttgacgaa1380
cttaccatgatttatatctgttggcaaaatgagacaatttattcatgttctgcgtatact1440
ttaatgatcatcgtattgcaacatgcttgtttaaccattatttatcaaacattacttttc1500
tctctacttgtgcacagtaaagcaggtgccatttgcttaacactaacaaaagctgtacaa1560
atactggggacggttccgaggtccgacgatcgtccgagttttcccttataaaagcgccgc1620
gatcgtaacgtaaagatcatcagtagaatttgctcttttccacagttcacaggtgaataa1680
acgatgaagcttgcctcctccgagaacgtcatcaccgagttcatgcgcttcaaggtgcgc1740
atggagggcaccgtgaacggccacgagttcgagatcgagggcgagggcgagggccgcccc1800
tacgagggccacaacaccgtgaagctgaaggtgaccaagggcggccccctgcccttcgcc1860
tgggacatcctgtccccccagttccagtacggctccaaggtgtacgtgaagcaccccgcc1920
gacatccccgactacaagaagctgtccttccccgagggcttcaagtgggagcgcgtgatg1980
aacttcgaggacggcggcgtggcgaccgtgacccaggactcctccctgcaggacggctgc2040
ttcatctacaaggtgaagttcatcggcgtgaacttcccctccgacggccccgtgatgcag2100
aagaagaccatgggctgggaggcctccaccgagcgcctgtacccccgcgacggcgtgctg2160
aagggcgagacccacaaggccctgaagctgaaggacggcggccactacctggtggagttc2220
aagtccatctacatggccaagaagcccgtgcagctgcccggctactactacgtggacgcc2280
aagctggacatcacctcccacaacgaggactacaccatcgtggagcagtacgagcgcacc2340
gagggccgccaccacctgttcctgagatctcgagcaccaccaccaccaccactaacctag2400
gtagctgagcgcatgcgatctcggcttcaaaacggtactggattttggattcaaacgaaa2460
gccatcgctacaacagaacaaataaaagaacattaatcaaaacgcataaaagatgggtta2520
attgtattcaataaggagaaaagtaattcctactagatagtttactatcacgcgaaagga2580
tggccagtcttcactacgggaagacaacctcgctgggaatcgaaactctgtcaacgctgg2640
aggtgccaacacatcttcgtaataaacatttttacatttatccaggcgtaaagaaacacg2700
atttagttatcaatttgtatttttggttcttatgaagaataaacttcttcaaattcactt2760
ccacgaatattccgtcccgttccgccagttccattcgagctc2802
- 还没有人留言评论。精彩留言会获得点赞!