提高植物营养组织油含量的转基因方法及表达载体和应用与流程
本发明属于基因工程技术领域,具体涉及提高植物营养组织油含量的转基因方法及表达载体和应用。
背景技术:
植物油用途广泛,不仅是食用油的主要来源,而且可用于动物饲料、肥皂、表面活性剂、化妆品、涂料、润滑油,以及生物柴油的生产。然而,由于人口的增长和可耕地面积的减少,在当前和今后很长的一段时间内,中国都将面临食用油和化工原油短缺的严峻局面。人们寄希望通过提高和改变油料植物的农艺和品质性状(其中包括种子产量、油脂的含量及其脂肪酸组分),使植物不仅是食用油的主要来源,而且还成为可持续地生产生物能源和化工原料的潜在工厂。
普遍认为,种子中油的生产涉及三个关键要素:(1)将光合产物有效地转化为脂肪酸;(2)将脂肪酸有效地掺入到甘油骨架上;(3)降低脂肪酸的降解。就此而言,油合成机器的主要元件也存在于营养器官中,这是因为:(1)作为油的主要组成成分,脂肪酸的主要合成部位是叶绿体或质体,而植物叶片富含叶绿体并提供脂肪酸合成所需的碳水化合物;(2)将脂肪酸组装到甘油骨架上形成油的酰基转移酶基因在营养器官中也有表达,这包括催化中性油脂三酰甘油合成的最后一步反应的二酰甘油酰基转移酶(dgat1)基因;(3)在某些逆境条件下或植物衰老过程中,叶片或茎杆中油的含量呈显著增加的趋势。事实上,叶等营养器官是可收获的生物质的主要组成部分,叶片尤其为脂肪酸的合成提供最主要的碳源,因而,如果油合成机器的元件运作正常,叶等营养器官或许是理想的油脂积累的场所。不过,叶在进化过程中演变为“源”组织,成为高度专化的碳水化合物合成和输出的器官,缺乏脂质积累的倾向。我们假定营养器官中油合成机器的元件组合搭配不当或运转效率低下是造成低含油量性状的一个主要原因之一,若能将控制种子油合成的上述三个关键遗传要素有机地整合到植物营养器官中,油合成与积累能力将会得到增强。
在经典的kennedy途径中,3-磷酸甘油酰基转移酶(gpat)、溶血磷脂酸酰基转移酶(lpaat)和acyl-coa:二酰甘油酰基转移酶(dgat)分别将脂肪酸组装到甘油的sn-1、sn-2和sn-3位置上,dgat被认为是参与种子油脂合成的关键限速酶,且发现衰老叶片中,此酶参与了tag的合成。一些研究致力于调查dgat基因在组成型表达的启动子(如35s)调控下对植物营养器官中油合成的影响,结果显示,atdgat1基因在烟草幼苗中的过表达可使其tag含量增至野生型的5.9倍,而叶片中,可高达野生型的7倍。
已有研究表明,在营养组织中过表达脂肪酸合成途径中的关键酶基因或转录因子,能加速光合产物相脂肪酸的转化以及油脂的合成。mendoza等在拟南芥中过表达参与种子成熟和油脂积累调控过程的转录因子leafycotyledon2(lec2),发现在营养组织中积累了种子特异的mrna,并且储存性tag含量明显增加。与此一致的是,以为表达35s强启动子驱动的lec2基因,可以有效提升拟南芥和烟草营养器官中的含油量。但与此同时,幼苗出现体细胞胚胎发生现象,且组织扭曲变形,影响转基因植株的正常生长。为解决这个问题,kim等尝试通过衰老诱导表达的方式,在拟南芥叶片中过表达lec2基因,其结果与野生型相比,转基因植株的tag含量增加了3倍,且未出现明显的生长异常。这说明,关键基因与合适启动子的有机结合对操控植物营养组织中油脂的合成和积累至关重要。但是,基于载体承受性和表达量的限制,选择何种基因组合并怎样合理地构建转录单元从而实现基因表达仍然是需要首先考虑和解决的技术问题。
酿酒酵母含有两个编码sn-1位的3-磷酸甘油酰基转移酶(gpat)基因gat1和gat2,催化甘油酯生物合成途径的第一步酰基化反应,虽然gat1和gat2同属于gpat家族基因,且酵母gat1p和gatp2多肽中存在保守酰基转移酶特征序列,但是,以酿酒酵母为模式生物,通过构建gat1和gat2的基因敲除或过表达体系,发现gat1和gat2基因对酵母的诸多生理影响存在明显差异。另外,oleosin蛋白在调节种子中脂质体稳定性方面具有重要作用,目前尚未将oleosin基因与其它基因组合在一起,在油料作物的营养器官中进行共表达的研究,
技术实现要素:
针对上述问题,本发明的目的在于提供提高植物营养组织油含量的转基因方法及表达载体和应用,该方法利用构建的表达载体,将其在植物营养组织中异位或异源表达,能显著提高植物营养组织中的油脂含量。
一种提高植物营养组织油含量的表达载体,含有由gat2、lec2、dgat1和oleo2四种基因组成的基因组合。
进一步的,所述gat2基因为来源于酿酒酵母的sct1-ybl011w,或与sct1-ybl011w核苷酸序列同源性达90%以上的基因,或编码的氨基酸序列与sct1-ybl011w氨基酸序列同源性达95%以上的基因。
进一步的,所述lec2基因为来源于拟南芥中的调控油脂积累的转录因子leafycotyledon2,或与该转录因子核苷酸序列同源性达90%以上的基因,或编码的氨基酸序列与该转录因子的氨基酸序列同源性达95%以上的基因。
进一步的,所述dgat1基因为来源于拟南芥的at2g19450,或与at2g19450核苷酸序列同源性达90%以上的基因,或编码的氨基酸序列与at2g19450氨基酸序列同源性达95%以上的基因。
进一步的,所述oleo2基因为来源于拟南芥的at5g40420,或与at5g40420核苷酸序列同源性达90%以上的基因,或编码的氨基酸序列与at5g40420氨基酸序列同源性达95%以上的基因。
更进一步的,所述表达载体中启动lec2基因表达的启动子为35s,终止该基因表达的终止子为nos;启动dgat1基因表达的启动子为35s,终止该基因表达的终止子为at4g25710基因的3’utr;启动oleo2基因表达的启动子为at4g25700基因的启动子,终止该基因表达的终止子为nos;启动gat2基因表达的启动子为35s,终止该基因表达的终止子为nos。
本发明还保护利用上述表达载体提高植物营养组织油含量的转基因方法,该方法包括以下步骤:
步骤一、构建所述表达载体;
步骤二、将表达载体进行根癌农杆菌转化,鉴定正确后获得阳性根癌农杆菌;
步骤三、取植物叶片外植体进行组织培养,用阳性根癌农杆菌浸染,筛选并继续培养至生根,移栽种植;或将植物培养至花期,用阳性根癌农杆菌浸染花序后进行暗培养,最终获得转基因阳性植株;
步骤四、取转基因阳性植株的叶片,进行分子鉴定和脂质分析,选择高油的转基因植株,成熟后收集种子,直至得到高油且稳定遗传的转基因株系。
本发明还保护上述表达载体在提高植物营养组织中油含量上的应用。
进一步的,所述植物为烟草、大豆、油菜、向日葵、花生、玉米或苜蓿。
本发明另外还保护上述表达载体在提高与植物营养组织中油合成与积累相关联的物质生产中的应用,其中,所述与植物营养组织中油合成与积累相关的物质生产为脂溶性物质的生产。
本发明的有益效果:
1、本发明选择四种来源于拟南芥或酵母中的参与油脂合成与积累不同过程的基因gat2、lec2、dgat1和oleo2,通过与强度不同的启动子连接,使相应的基因在启动子的操控下,在植物营养组织中异位或异源表达,有效诱导营养细胞向胚性细胞转变,并通过提高营养细胞中合成油脂的酰基转移酶的活性和降低降解油脂的脂酶活性,使营养器官中油脂含量得到增加,最后筛选得到使植株营养组织内高油的基因组合,为创建在植物营养组织中生产植物油的体系提供分子手段。
2、本发明将四个关键要素的基因组合在一起,构建植物表达载体,转化到植物组织中,使植物营养组织中油的生产能力显著提高。以烟草为研究材料,筛选得到的10株高油植株中,与野生型相比,tag含量最高可增加21.59倍。该套体系有望应用到例如大豆、油菜、花生等植物中提高其营养组织中油含量或提高部分脂溶性物质的生产。
附图说明
图1是载体pbi121-35smcs的构建流程图谱;
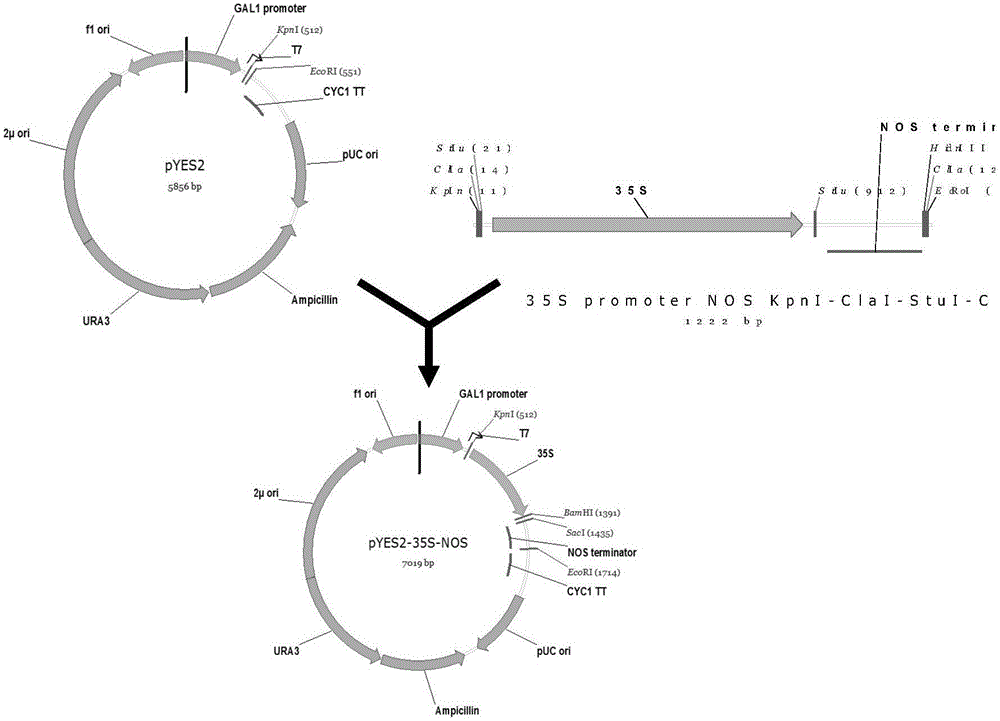
图2是重组载体pyes2-35s-nos的构建流程图谱;
图3是重组载体pyes2-35s-3’utr-bch1-5’utr-nos的构建流程图谱;
图4是重组载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos的构建流程图谱;
图5是重组载体pyes2-dgat1-oleo2的构建流程图谱;
图6是重组载体pbi12135s-gat2的构建流程图谱;
图7是重组载体pbi121-lec2的构建流程图谱;
图8是重组载体pbi121-dgat1-oleo2-gat2的构建流程图;
图9重组载体pbi121-lec2-dgat1-oleo2-gat2的构建流程图谱;
图10是重组载体pbi121-lec2-dgat1-oleo2-gat2的酶切鉴定图;泳道1:stui酶切;m:1kbdnaladder;
图11是重组载体pbi121-lec2-dgat1-oleo2-gat2的pcr鉴定图;泳道1:目的片段lec2-dgat1;m:1kbdnaladder;
图12是烟草再生过程示意图;
图13是转基因烟草中三酰甘油含量;wt:野生拟南芥;6-3,6-9,6-10,6-11,6-12,6-18,6-19,6-20,6-21,6-24:pbi121-lec2-dgat1-oleo2-gat2载体的高油植株;
图14是植物双元载体的构建技术路线图。
具体实施方式
下面通过具体的实施例对本发明作进一步的解释说明。
实施例:
1、转录单元的构建和目的基因的筛选
为了构建不同的植物转录单元,本研究选择可以在营养器官中组成性表达的35s和bch1作为启动子,nos作为终止子。此外,还选择参与油脂合成的目的基因:(i)酵母中编码3-磷酸甘油酰基转移酶的基因gat2,(ii)编码二酰甘油酰基转移酶的一个基因(dgat1),前者和后者分别参与油脂合成的第一步和第三步酰化反应;(iii)oleosin2(oleo2)编码油体嵌合蛋白,可维持油滴的完整性和稳定性;(iv)将营养细胞转变为胚性细胞的调控因子lec2,其在叶片中异位表达能显著增加叶片油的合成和积累。
2、目的基因的克隆
2.1酵母gat2的克隆
以酵母基因组为模板,用引物gat2fpbamhi和gat2rpxhoi扩增gat2(基因序列如seqidno:1所示,编码的氨基酸序列如seqidno:5所示),于gat2的5’端引入酶切位点bamhi,3’端引入酶切位点xhoi,凝胶电泳观察约2200bp的亮带,回收,获得目的基因gat2(sct1-ybl011w)-bamhi-xhoi。
2.2拟南芥oleo2、dgat1和lec2的克隆
提取拟南芥总rna,反转录形成cdna,以拟南芥的cdna为模板,分别用引物zzf60(oleo2fp)和zzf61(oleo2rp),zzf64(dgat1fp)和zzf65(dgat1rp),zzf68(lec2fp)和zzf69(lec2rp)进行pcr扩增,获得oleo2(872bp)、dgat1(1591)和lec2(1116bp)。其中,oleo2的基因序列如seqidno:3所示,其编码的氨基酸序列如seqidno:7所示;dgat1的基因序列如seqidno:2所示,其编码的氨基酸序列如seqidno:6所示;lec2的基因序列如seqidno:4所示,其编码的氨基酸序列如seqidno:8所示。然后以纯化回收产物为模板,分别用引物zzf62(oleo2fp-saci)和zzf63(oleo2rp-saci),zzf66(dgat1fp-bamhi)和zzf67(dgat1rp-bamhi),zzf70(lec2fp-xbai)和zzf71(lec2rp-saci)进行pcr扩增,分别在5’末端和3’末端加上单酶切位点,最终获得带有酶切位点的目的基因oleo2(at5g40420)-saci-saci、dgat1(at2g19450)-bamhi-bamhi和lec2-xbai-saci。
3、启动子bch1的克隆
β-胡萝卜素羟化酶(bch1)基因即3’utr-bch1-5’utr,扩增此片段是为了引入启动子和终止子。以拟南芥基因组为模板,用引物zzf56(bch1fp)和zzf57(bch1rp)进行pcr扩增,然后以纯化回收产物为模板,用引物zzf58(bch1fp-bamhi)和zzf59(bch1rp-saci)再次pcr扩增出一条2504bp的亮条带,回收,获得带有酶切位点的目的基因bchi-bamhi-saci。
4、载体的改造
4.1双元载体pbi121-35smcs的改造
以质粒pbi121-gus为模板,用引物zzf47(35spromoterfp)和zzf48(35spromoterrp)进行pcr扩增,获得35spromoter。然后以35spromoter为模板,分别用3对引物zzf47(35spromoterfp)和zzf49(35spromoterrpmcs1),zzf47(35spromoterfp)和zzf50(35spromoterrpmcs2),zzf47(35spromoterfp)和zzf51(35spromoterrpmcs3)依次对其纯化回收产物进行pcr扩增,凝胶电泳观察到一条约1000bp的亮条带,回收,最终获得目的基因35s-mcs。其中多克隆位点包括bamhi,xmai,smai,xhoi和saci。通过酶切位点hindiii和saci将目的基因35smcs插入到载体pbi121-gus中,如图图1所示,然后进行转化,培养,提取质粒。分别用clai、ecori和hindiii、saci酶切提取的双元载体pbi121-35smcs,将酶切产物进行凝胶电泳,酶切的片段分别为1595bp、11313bp和915bp、11993bp,验证正确,且经测序验证后,获得新的双元载体pbi121-35smcs。
4.2中间载体pyes2-35s-nos的改造
以pbi121-35smcs为模板,用引物zzf52(35sfp)和zzf53(nosrp)进行pcr扩增,获得35s-nos。然后以纯化回收的35s-nos-t为模板,用引物zzf54(35sfp-kpni-clai-stui)和zzf55(nos-t-hindiii-clai-ecori)进行pcr扩增,在5’端和3’端加入多酶切位点,最终获得一条约1600bp的亮条带,回收,获得目的基因35s-nos。通过酶切位点kpni和ecori将目的基因35s-nos插入到载体pyes2中,如图图2所示,转化,培养,提取质粒,再经酶切和测序验证正确后,从而获得中间载体pyes2-35s-nos。
4.3中间载体pyes2-35s-3’utr-bch1-5’utr-nos的改造
以拟南芥基因组dna为模板,用引物zzf56(bch1fp)和zzf57(bch1rp)进行pcr扩增,获得3’utr-bch1-5’utr。其中,3’utr为at4g25710基因的终止子,5’utr为at4g25700基因的启动子。然后以纯化回收的3’utr-bch1-5’utr为模板,用引物zzf58(bch1fp-bamhi)和zzf59(bch1rp-saci)进行pcr扩增,在5’端和3’端加入bamhi、saci酶切位点。通过酶切位点bamhi和saci将目的基因3’utr-bch1-5’utr插入到载体pyes2-35smcs-nos,验证正确,从而获得中间载体pyes2-35s-3’utr-bch1-5’utr-nos,如图3所示。
分别用kpni和ecori,bamhi和saci对pyes2-35s-3’utr-bch1-5’utr-nos载体进行双酶切,将酶切产物进行凝胶电泳,酶切的片段分别为3662bp和5817bp,2504bp和6975bp,正确。且经测序验证,序列正确。
5、中间载体的构建
5.1中间载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos的构建
通过酶切位点saci将目的基因oleo2-saci-saci插入到载体pyes2-35s-3’utr-bch1-5’utr-nos,获得中间载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos,如图4所示。
需要注意的是:由于载体pyes2-35s-3’utr-bch1-5’utr-nos是由saci单酶切获得的,为防止载体自连,需对载体片段去磷酸化。然后用pcr产物纯化试剂盒纯化回收。
载体验证:分别用saci,ecori和saci酶切载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos,将酶切产物进行凝胶电泳,酶切的片段分别为880bp、9229bp和630bp、9479bp。以pyes2-35s-3’utr-bch1-5’utr-oleo2-nos为模板,zzf56(bch1fp)和zzf61(oleo2rp)为引物,pcr扩增出一条3105bp的亮条带,来验证其方向性。且经测序验证,序列正确。
5.2中间载体pyes2-dgat1-oleo2的构建
通过酶切位点bamhi将目的基因dgat1-bamhi-bamhi插入到载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos,最终获得中间载体pyes2-35s-3’utr-dgat1-bch1-5’utr-oleo2-nos,即pyes2-dgat1-oleo2,如图5所示。
载体pyes2-35s-3’utr-bch1-5’utr-oleo2-nos是由bamhi单酶切获得的,为防止载体自连,需对载体片段去磷酸化。然后用pcr产物纯化试剂盒纯化回收。
载体验证:用bamhi酶切载体pyes2-dgat1-oleo2,将酶切产物进行凝胶电泳,酶切的片段为1575bp、10109bp。以pyes2-dgat1-oleo2为模板,zzf52(35sfp)和zzf65(dgat1rp)为引物,pcr扩增出一条2408bp的亮条带,来验证其方向性。且经测序验证,序列正确。
6、双元表达载体的构建
6.1技术路线(如图14所示)
6.2单基因表达载体的构建
6.2.1单基因表达载体pbi12135s-gat2的构建
通过双酶切位点bamhi和xhoi将目的基因gat2-bamhi-xhoi插入双元载体pbi121-35smcs,构成单基因表达载体pbi12135s-gat2,构建图谱如图6所示,然后进行大肠杆菌感受态dh5α转化,并进行酶切验证和基因测序。
6.2.2单基因表达载体pbi121-lec2的构建
通过双酶切位点xbai和saci将目的基因lec2-xbai-saci插入双元载体pbi121-35smcs,构成单基因表达载体pbi121-lec2,构建图谱如图7所示,然后进行大肠杆菌感受态dh5α转化,并进行酶切验证和基因测序。
载体验证:分别用bamhi,xhoi和saci,xbai酶切载体pbi12135s-gat2,将酶切产物进行凝胶电泳,酶切的片段分别为646bp、13316bp和1104bp、12858bp。且经测序验证,序列正确。
6.3三基因表达载体pbi121-dgat1-oleo2-gat2的构建
通过酶切位点clai将目的片段dgat1-oleo2从载体pyes2-dgat1-oleo2上切下,然后插入单基因表达载体pbi121-gat2,构成三基因表达载体pbi121-dgat1-oleo2-gat2,构建图谱如图8所示。由于单基因表达载体pbi121-gat2本身含有两个相同酶切位点clai,采用不完全酶切的方法获得载体片段。
载体验证:用clai酶切载体pbi121-dgat1-oleo2-gat2,将酶切产物进行凝胶电泳,酶切的片段为3118bp、5859bp、12053bp。且经测序验证,序列正确;用stui,noti酶切pbi121-dgat1-oleo2-gat2,将酶切产物进行凝胶电泳,酶切的片段为4640bp和16390bp;以pbi121-dgat1-oleo2-gat2为模板,gat2fpbamhi和gat2rpxhoi为引物,pcr扩增出一条2295bp的亮条带。载体验证正确。
6.4四基因表达载体的构建
6.4.1lec2基因扩增
以单基因表达载体pbi121-lec2为模板,用引物zzf72(lec2ptufp)和zzf73(lec2pturp)进行pcr扩增,然后以纯化回收产物为模板,用引物zzf74(lec2ptufp-stui)和zzf75(lec2pturp-stui)再次进行pcr扩增,得一条2249bp的亮条带,回收,获得lec2ptu-stui-stui。
6.4.2载体构建
利用stui分别酶切lec2ptu-stui-stui和pbi121-dgat1-oleo2-gat2,回收酶切产物。其中,而对于≥20kb的载体片段,回收时易使载体片段发生机械损伤,出现拖带现象,因此需要对去磷酸化的载体片段进行抽提,以去除去磷酸化反应混合物。然后将回收的lec2ptu-stui-stui和pbi121-dgat1-oleo2-gat2基因片段进行连接,最终获得四基因表达载体pbi121-lec2-dgat1-oleo2-gat2,构建图谱如图9所示。
6.4.3载体验证
图10所示,用stui酶切载体pbi121-lec2-dgat1-oleo2-gat2,将酶切产物进行凝胶电泳,酶切的片段分别为2234bp、21030bp。且经测序验证,序列正确。图11所示,以pbi121-lec2-dgat1-oleo2-gat2为模板,zzf68(lec2fp)和zzf65(dgat1rp)为引物,pcr扩增出一条3808bp的亮条带。
7、根癌农杆菌gv3101的转化与鉴定
制备根癌农杆菌gv3101感受态,将植物表达载体pbi121-lec2-dgat1-oleo2-gat2进行根癌农杆菌的转化,然后再提取根癌农杆菌中的质粒,并对其进行酶切或pcr验证。
8、烟草的遗传转化
以大田栽培品种k326的叶片作为外植体,通过根瘤农杆菌介导法,将植物表达载体pbi121-lec2-dgat1-oleo2-gat2导入烟草中,经过50μg/ml卡那霉素(kan)筛选,获得转基因烟草植株。
具体转化步骤为:取温室中生长约2个月的k326幼嫩叶片,进行表面消毒,放于1/2ms培养基上,暗处,25±1℃预培养2-3天。农杆菌(已转入植物表达载体pbi121-lec2-dgat1-oleo2-gat2侵染后黑暗条件下共培养2天,然后将叶片转移到筛选培养基上,25±1℃,16h光照,8h黑暗,培养40天,将芽切下转入生根培养基中,14天后获得转基因烟草植株,如图12所示。
9、转基因烟草的筛选鉴定
9.1t0代转基因烟草的分子鉴定
以提取的转基因烟草pbi121-lec2-dgat1-oleo2-gat2的基因组dna为模板,用引物zzf47(35spromoterfp)和zzf48(35spromoterrp),gat2fp和gat2rp,zzf52(35sfp)和zzf65(dgat1rp),zzf56(bch1fp)和zzf61(oleo2rp),zzf68(lec2fp)和zzf65(dgat1rp)pcr扩增插入片段35s,gat2,35s-dgat1,bch1-oleo2和lec2-nos进行pcr验证,片段大小分别为911bp,2295bp,2431bp,3125bp和3808bp。结果可知,26株转基因植株中有15株能同时扩增出5个外源目的基因片段,阳性率为57.69%。
9.2t0代转基因烟草的脂类分析
提取t0代转基因烟草植株pbi121-lec2-dgat1-oleo2-gat2叶片中的脂质,用薄层色谱法分离三酰甘油,然后用气相色谱法分析三酰甘油中的脂肪酸组分及相对含量。
结果可知,15株阳性转化植株中,筛选出10株高油植株6-3、6-9、6-10、6-11、6-12、6-18、6-19、6-20、6-21、6-24。与野生相比,tag的含量分别增加9.92、18.16、21.13、18.71、7.86、17.56、21.59、9.16、20.01、17.07倍,如图13所示。
上述实施例中用到的引物及其核苷酸序列如下表1所示。
表1:引物及核苷酸序列表
由此可见,本发明所述lec2、dgat1、oleo2和gat2的基因组合,在合适的启动子作用下,对油合成、积累和降解过程中的关键因子进行调控,基因间协同表达和作用,能够显著提高拟南芥或烟草营养组织中的油脂含量,可将此方法应用于大豆、油菜、花生或玉米等植物中,有望促进生物燃料的生产;或将其应用于苜蓿、高粱等饲料作物中提高饲料的营养。
需要说明的是,以上所述的实施例应理解为说明性的,而非限制本发明的保护范围,对于本领域技术人员而言,在不背离本发明实质和范围的前提下,对本发明作出的一些非本质的改进和调整仍属于本发明的保护范围。
sequencelisting
<110>浙江农林大学
<120>提高植物营养组织油含量的转基因方法及表达载体和应用
<130>1
<160>8
<170>patentinversion3.3
<210>1
<211>2280
<212>dna
<213>酿酒酵母
<400>1
atgcctgcaccaaaactcacggagaaatttgcctcttccaagagcacacagaaaactacg60
aattacagttccatcgaggccaaaagcgtcaagacgtcggctgatcaggcatacatctac120
caagagcctagcgctaccaagaagatactttactccatcgccacatggctgttgtacaac180
atcttccactgcttctttagagaaatcagaggccggggcagtttcaaggtaccgcaacag240
ggaccggtgatctttgttgcggctccgcatgctaaccagttcgtcgaccctgtaatcctt300
atgggcgaggtgaagaaatctgtcaacagacgtgtgtccttcttgattgcggagagctca360
ttaaagcaaccccccatagggtttttggctagtttcttcatggccataggcgtggtaagg420
ccgcaggataatttgaaaccggcagaaggtactatccgcgtagatccaacagactacaag480
agagttatcggccacgacacgcatttcttgactgattgtatgccaaagggtctcatcggg540
ttacccaaatcaatgggatttggagaaatccagtccatagaaagtgacacgagtttgacc600
ctaagaaaagagttcaaaatggccaaaccagagattaaaactgctttactcaccggcact660
acttataaatatgccgctaaagtcgaccaatcttgcgtttaccatagagtttttgagcat720
ttggcccataacaactgcattgggatctttcctgaaggtgggtcccacgacagaacaaac780
ttgttgcccctgaaagcaggtgtggcgattatggctcttggttgcatggataagcatcct840
gacgtcaatgttaagattgttccctgcggtatgaattatttccatccacataagttcagg900
tcgagagcggttgttgaattcggtgaccccattgaaataccgaaggaactagtcgccaag960
taccacaacccggaaacgaacagagatgcagtgaaagaattattagataccatatcgaag1020
ggtttacaatccgttaccgttacatgttctgattatgaaactttgatggtggttcaaacg1080
ataagaagactatatatgacacaatttagcaccaagttaccgttgcccttgattgtggaa1140
atgaacagaagaatggtcaaaggttacgaattctatagaaacgatcctaaaatagcggac1200
ttgaccaaagatataatggcatataatgccgccttgagacactataatcttcctgatcac1260
cttgtggaggaggcaaaggtaaatttcgcaaaaaacctcggacttgttttttttagatcc1320
atcgggctctgcatcctcttttcgttagccatgccaggtatcattatgttctcacctgtc1380
ttcatattagccaagagaatttctcaagaaaaggcccgtaccgctttgtccaagtctaca1440
gttaaaataaaggctaacgatgtcattgccacgtggaaaatcttgattgggatgggattt1500
gcgcccttgctttacatcttttggtccgttttaatcacttattacctcagacataaacca1560
tggaataaaatatatgttttttccgggtcttacatctcgtgtgttatagtcacgtattcc1620
gccttaatcgtgggtgatattggtatggatggtttcaaatctttgagaccactggtttta1680
tctcttacatctccaaagggcttgcaaaagctacaaaaggatcgtagaaatctggcagaa1740
agaataatcgaagttgtaaataactttggaagcgaattattccccgatttcgatagtgcc1800
gccctacgtgaagaattcgacgtcatcgatgaagaggaagaagatcgaaaaacctcagaa1860
ttgaatcgcaggaaaatgctaagaaaacagaaaataaaaagacaagaaaaagattcgtca1920
tcacctatcatcagccaacgtgacaaccacgatgcctatgaacaccataaccaagattcc1980
gatggcgtctcattggtcaatagtgacaattccctctctaacattccattattctcttct2040
acttttcatcgtaagtcagagtcttccttagcttcgacatccgttgcaccttcttcttcc2100
tccgaatttgaggtagaaaacgaaatcttggaggaaaaaaatggattagcaagtaaaatc2160
gcacaggccgtcttaaacaagagaattggtgaaaatactgccagggaagaggaagaggaa2220
gaagaagaggaagaagaagaagaggaagaagaagaagaagggaaagaaggagatgcgtag2280
<210>2
<211>1591
<212>dna
<213>拟南芥
<400>2
cttctggatccttcgaaatggcgattttggattctgctggcgttactacggtgacggaga60
acggtggcggagagttcgtcgatcttgataggcttcgtcgacggaaatcgagatcggatt120
cttctaacggacttcttctctctggttccgataataattctccttcggatgatgttggag180
ctcccgccgacgttagggatcggattgattccgttgttaacgatgacgctcagggaacag240
ccaatttggccggagataataacggtggtggcgataataacggtggtggaagaggcggcg300
gagaaggaagaggaaacgccgatgctacgtttacgtatcgaccgtcggttccagctcatc360
ggagggcgagagagagtccacttagctccgacgcaatcttcaaacagagccatgccggat420
tattcaacctctgtgtagtagttcttattgctgtaaacagtagactcatcatcgaaaatc480
ttatgaagtatggttggttgatcagaacggatttctggtttagttcaagatcgctgcgag540
attggccgcttttcatgtgttgtatatccctttcgatctttcctttggctgcctttacgg600
ttgagaaattggtacttcagaaatacatatcagaacctgttgtcatctttcttcatatta660
ttatcaccatgacagaggttttgtatccagtttacgtcaccctaaggtgtgattctgctt720
ttttatcaggtgtcactttgatgctcctcacttgcattgtgtggctaaagttggtttctt780
atgctcatactagctatgacataagatccctagccaatgcagctgataaggccaatcctg840
aagtctcctactacgttagcttgaagagcttggcatatttcatggtcgctcccacattgt900
gttatcagccaagttatccacgttctgcatgtatacggaagggttgggtggctcgtcaat960
ttgcaaaactggtcatattcaccggattcatgggatttataatagaacaatatataaatc1020
ctattgtcaggaactcaaagcatcctttgaaaggcgatcttctatatgctattgaaagag1080
tgttgaagctttcagttccaaatttatatgtgtggctctgcatgttctactgcttcttcc1140
acctttggttaaacatattggcagagcttctctgcttcggggatcgtgaattctacaaag1200
attggtggaatgcaaaaagtgtgggagattactggagaatgtggaatatgcctgttcata1260
aatggatggttcgacatatatacttcccgtgcttgcgcagcaagataccaaagacactcg1320
ccattatcattgctttcctagtctctgcagtctttcatgagctatgcatcgcagttcctt1380
gtcgtctcttcaagctatgggcttttcttgggattatgtttcaggtgcctttggtcttca1440
tcacaaactatctacaggaaaggtttggctcaacggtggggaacatgatcttctggttca1500
tcttctgcattttcggacaaccgatgtgtgtgcttctttattaccacgacctgatgaacc1560
gaaaaggatctatgtcatgaggatccactaa1591
<210>3
<211>872
<212>dna
<213>拟南芥
<400>3
attacaaagaaaataggtaaaaacaatttctcattagcttacaatggcggatacacaccg60
tgtcgaccgtactgatagacactttcaatttcagtcgccctatgaaggcggccgaggtca120
aggtcagtatgaaggtgaccgtggttacggtggtggcggttacaagagcatgatgcctga180
aagtggcccatctagtacccaagtattgtccctgttgattggagtccctgtcgtcggttc240
gctacttgccttggctggattacttctagctggttcggtgatcggcttaatggttgcttt300
accactatttctcctcttcagcccggttatagtcccagcggctctaactatcgggcttgc360
aatgacaggctttttagcctcggggatgttcggtctaaccgggcttagctcaatctcatg420
ggtcatgaactatcttcgtgggacaaggagaactgtgcctgagcaattggagtatgctaa480
gaggagaatggctgatgcggttggctacgcaggacaaaagggcaaagaaatgggccagca540
tgtgcagaacaaggcccaagatgttaaacaatatgatatttctaagccacatgacactac600
cactaagggtcatgagactcaggggaggacgacggctgcatgatgagttttcagtatgaa660
cggtagatatgtgttttcactattatgtcgttttttctgcattttcaatatgatgttatg720
tgttttttttgtttggctttttgttgaaccgtgtatgtgttttatgtttttgtaagcatg780
aaagatcgcaagtgttgtggtaatatttgaatgtaataatatgataagttgataaatcat840
gggaacatttaaattaggtggacatgtttagc872
<210>4
<211>2249
<212>dna
<213>拟南芥
<400>4
attgaaggcctgcaggtccccagattagccttttcaatttcagaaagaatgctaacccac60
agatggttagagaggcttacgcagcaggtctcatcaagacgatctacccgagcaataatc120
tccaggaaatcaaataccttcccaagaaggttaaagatgcagtcaaaagattcaggacta180
actgcatcaagaacacagagaaagatatatttctcaagatcagaagtactattccagtat240
ggacgattcaaggcttgcttcacaaaccaaggcaagtaatagagattggagtctctaaaa300
aggtagttcccactgaatcaaaggccatggagtcaaagattcaaatagaggacctaacag360
aactcgccgtaaagactggcgaacagttcatacagagtctcttacgactcaatgacaaga420
agaaaatcttcgtcaacatggtggagcacgacacacttgtctactccaaaaatatcaaag480
atacagtctcagaagaccaaagggcaattgagacttttcaacaaagggtaatatccggaa540
acctcctcggattccattgcccagctatctgtcactttattgtgaagatagtggaaaagg600
aaggtggctcctacaaatgccatcattgcgataaaggaaaggccatcgttgaagatgcct660
ctgccgacagtggtcccaaagatggacccccacccacgaggagcatcgtggaaaaagaag720
acgttccaaccacgtcttcaaagcaagtggattgatgtgatatctccactgacgtaaggg780
atgacgcacaatcccactatccttcgcaagacccttcctctatataaggaagttcatttc840
atttggagagaacacgggggactctagaaaatggataacttcttaccctttccctcttct900
aacgcaaactctgtccaagaactctctatggatcctaacaacaatcgctcgcacttcaca960
acagtccctacttatgatcatcatcaggctcagcctcatcacttcttgcctccgttttca1020
tacccggtggagcagatggcggcggtgatgaatcctcagccggtttacttatcggagtgt1080
tatcctcagatcccggttacgcaaaccggaagtgaattcggttctctggttggtaatcct1140
tgtttgtggcaagagagaggtggttttcttgatccgcgtatgacgaagatggcaaggatc1200
aacaggaaaaacgccatgatgagatcaagaaacaactctagccctaattctagtccaagt1260
gagttggttgattcaaagagacagctgatgatgcttaacttgaaaaataacgtgcagatc1320
tccgacaagaaagatagctaccaacagtccacatttgataacaagaagcttagggttttg1380
tgtgagaaggaattgaagaacagcgatgttgggtcactcgggaggatagttctaccaaag1440
agagatgcagaagcaaatcttccgaagctatctgataaagaaggaatcgttgtacagatg1500
agagatgttttctctatgcagtcttggtctttcaaatacaagttttggtccaataacaag1560
agcagaatgtatgtcctcgagaacacaggagaatttgtgaagcaaaatggagctgagata1620
ggagactttttaacaatatacgaggacgaaagcaagaatctctacttcgccatgaatgga1680
aattcgggaaaacaaaatgaaggaagagaaaatgagtcgagggaaaggaaccactacgaa1740
gaggcaatgcttgattacataccaagagacgaagaggaagcttccattgcaatgctcatc1800
ggaaatctaaacgatcactatcccatccctaacgatctcatggacctcaccactgacctt1860
cagcaccatcaagccacgtcctcatcaatgccacctgaggatcacgcgtacgtgggttca1920
tccgatgatcaggtgagctttaacgactttgagtggtggtgagagctcgaatttccccga1980
tcgttcaaacatttggcaataaagtttcttaagattgaatcctgttgccggtcttgcgat2040
gattatcatataatttctgttgaattacgttaagcatgtaataattaacatgtaatgcat2100
gacgttatttatgagatgggtttttatgattagagtcccgcaattatacatttaatacgc2160
gatagaaaacaaaatatagcgcgcaaactaggataaattatcgcgcgcggtgtcatctat2220
gttactagatcgggaattcaggcctaatg2249
<210>5
<211>759
<212>prt
<213>酿酒酵母
<400>5
metproalaprolysleuthrglulysphealaserserlysserthr
151015
glnlysthrthrasntyrserserileglualalysservallysthr
202530
seralaaspglnalatyriletyrglngluproseralathrlyslys
354045
ileleutyrserilealathrtrpleuleutyrasnilephehiscys
505560
phephearggluileargglyargglyserphelysvalproglngln
65707580
glyprovalilephevalalaalaprohisalaasnglnphevalasp
859095
provalileleumetglygluvallyslysservalasnargargval
100105110
serpheleuilealagluserserleulysglnproproileglyphe
115120125
leualaserphephemetalaileglyvalvalargproglnaspasn
130135140
leulysproalagluglythrileargvalaspprothrasptyrlys
145150155160
argvalileglyhisaspthrhispheleuthraspcysmetprolys
165170175
glyleuileglyleuprolyssermetglypheglygluileglnser
180185190
ilegluseraspthrserleuthrleuarglysgluphelysmetala
195200205
lysprogluilelysthralaleuleuthrglythrthrtyrlystyr
210215220
alaalalysvalaspglnsercysvaltyrhisargvalphegluhis
225230235240
leualahisasnasncysileglyilepheprogluglyglyserhis
245250255
aspargthrasnleuleuproleulysalaglyvalalailemetala
260265270
leuglycysmetasplyshisproaspvalasnvallysilevalpro
275280285
cysglymetasntyrphehisprohislyspheargserargalaval
290295300
valglupheglyaspproilegluileprolysgluleuvalalalys
305310315320
tyrhisasnprogluthrasnargaspalavallysgluleuleuasp
325330335
thrileserlysglyleuglnservalthrvalthrcysserasptyr
340345350
gluthrleumetvalvalglnthrileargargleutyrmetthrgln
355360365
pheserthrlysleuproleuproleuilevalglumetasnargarg
370375380
metvallysglytyrgluphetyrargasnaspprolysilealaasp
385390395400
leuthrlysaspilemetalatyrasnalaalaleuarghistyrasn
405410415
leuproasphisleuvalgluglualalysvalasnphealalysasn
420425430
leuglyleuvalphepheargserileglyleucysileleupheser
435440445
leualametproglyileilemetpheserprovalpheileleuala
450455460
lysargileserglnglulysalaargthralaleuserlysserthr
465470475480
vallysilelysalaasnaspvalilealathrtrplysileleuile
485490495
glymetglyphealaproleuleutyrilephetrpservalleuile
500505510
thrtyrtyrleuarghislysprotrpasnlysiletyrvalpheser
515520525
glysertyrilesercysvalilevalthrtyrseralaleuileval
530535540
glyaspileglymetaspglyphelysserleuargproleuvalleu
545550555560
serleuthrserprolysglyleuglnlysleuglnlysaspargarg
565570575
asnleualagluargileilegluvalvalasnasnpheglyserglu
580585590
leupheproasppheaspseralaalaleuarggluglupheaspval
595600605
ileaspglugluglugluasparglysthrsergluleuasnargarg
610615620
lysmetleuarglysglnlysilelysargglnglulysaspserser
625630635640
serproileileserglnargaspasnhisaspalatyrgluhishis
645650655
asnglnaspseraspglyvalserleuvalasnseraspasnserleu
660665670
serasnileproleupheserserthrphehisarglyssergluser
675680685
serleualaserthrservalalaproserserserserglupheglu
690695700
valgluasngluileleugluglulysasnglyleualaserlysile
705710715720
alaglnalavalleuasnlysargileglygluasnthralaargglu
725730735
gluglugluglugluglugluglugluglugluglugluglugluglu
740745750
gluglylysgluglyaspala
755
<210>6
<211>520
<212>prt
<213>拟南芥
<400>6
metalaileleuaspseralaglyvalthrthrvalthrgluasngly
151015
glyglygluphevalaspleuaspargleuargargarglysserarg
202530
seraspserserasnglyleuleuleuserglyseraspasnasnser
354045
proseraspaspvalglyalaproalaaspvalargaspargileasp
505560
servalvalasnaspaspalaglnglythralaasnleualaglyasp
65707580
asnasnglyglyglyaspasnasnglyglyglyargglyglyglyglu
859095
glyargglyasnalaaspalathrphethrtyrargproservalpro
100105110
alahisargargalaarggluserproleuserseraspalailephe
115120125
lysglnserhisalaglyleupheasnleucysvalvalvalleuile
130135140
alavalasnserargleuileilegluasnleumetlystyrglytrp
145150155160
leuileargthraspphetrppheserserargserleuargasptrp
165170175
proleuphemetcyscysileserleuserilepheproleualaala
180185190
phethrvalglulysleuvalleuglnlystyrilesergluproval
195200205
valilepheleuhisileileilethrmetthrgluvalleutyrpro
210215220
valtyrvalthrleuargcysaspseralapheleuserglyvalthr
225230235240
leumetleuleuthrcysilevaltrpleulysleuvalsertyrala
245250255
histhrsertyraspileargserleualaasnalaalaasplysala
260265270
asnprogluvalsertyrtyrvalserleulysserleualatyrphe
275280285
metvalalaprothrleucystyrglnprosertyrproargserala
290295300
cysilearglysglytrpvalalaargglnphealalysleuvalile
305310315320
phethrglyphemetglypheileilegluglntyrileasnproile
325330335
valargasnserlyshisproleulysglyaspleuleutyralaile
340345350
gluargvalleulysleuservalproasnleutyrvaltrpleucys
355360365
metphetyrcysphephehisleutrpleuasnileleualagluleu
370375380
leucyspheglyasparggluphetyrlysasptrptrpasnalalys
385390395400
servalglyasptyrtrpargmettrpasnmetprovalhislystrp
405410415
metvalarghisiletyrpheprocysleuargserlysileprolys
420425430
thrleualaileileilealapheleuvalseralavalphehisglu
435440445
leucysilealavalprocysargleuphelysleutrpalapheleu
450455460
glyilemetpheglnvalproleuvalpheilethrasntyrleugln
465470475480
gluargpheglyserthrvalglyasnmetilephetrppheilephe
485490495
cysilepheglyglnprometcysvalleuleutyrtyrhisaspleu
500505510
metasnarglysglysermetser
515520
<210>7
<211>199
<212>prt
<213>拟南芥
<400>7
metalaaspthrhisargvalaspargthrasparghispheglnphe
151015
glnserprotyrgluglyglyargglyglnglyglntyrgluglyasp
202530
argglytyrglyglyglyglytyrlyssermetmetproglusergly
354045
proserserthrglnvalleuserleuleuileglyvalprovalval
505560
glyserleuleualaleualaglyleuleuleualaglyservalile
65707580
glyleumetvalalaleuproleupheleuleupheserprovalile
859095
valproalaalaleuthrileglyleualametthrglypheleuala
100105110
serglymetpheglyleuthrglyleuserserilesertrpvalmet
115120125
asntyrleuargglythrargargthrvalprogluglnleuglutyr
130135140
alalysargargmetalaaspalavalglytyralaglyglnlysgly
145150155160
lysglumetglyglnhisvalglnasnlysalaglnaspvallysgln
165170175
tyraspileserlysprohisaspthrthrthrlysglyhisgluthr
180185190
glnglyargthrthralaala
195
<210>8
<211>362
<212>prt
<213>拟南芥
<400>8
metaspasnpheleupropheproserserasnalaasnservalgln
151015
gluleusermetaspproasnasnasnargserhisphethrthrval
202530
prothrtyrasphishisglnalaglnprohishispheleupropro
354045
phesertyrprovalgluglnmetalaalavalmetasnproglnpro
505560
valtyrleuserglucystyrproglnileprovalthrglnthrgly
65707580
serglupheglyserleuvalglyasnprocysleutrpglngluarg
859095
glyglypheleuaspproargmetthrlysmetalaargileasnarg
100105110
lysasnalametmetargserargasnasnserserproasnserser
115120125
prosergluleuvalaspserlysargglnleumetmetleuasnleu
130135140
lysasnasnvalglnileserasplyslysaspsertyrglnglnser
145150155160
thrpheaspasnlyslysleuargvalleucysglulysgluleulys
165170175
asnseraspvalglyserleuglyargilevalleuprolysargasp
180185190
alaglualaasnleuprolysleuserasplysgluglyilevalval
195200205
glnmetargaspvalphesermetglnsertrpserphelystyrlys
210215220
phetrpserasnasnlysserargmettyrvalleugluasnthrgly
225230235240
gluphevallysglnasnglyalagluileglyasppheleuthrile
245250255
tyrgluaspgluserlysasnleutyrphealametasnglyasnser
260265270
glylysglnasngluglyarggluasngluserarggluargasnhis
275280285
tyrgluglualametleuasptyrileproargaspgluglugluala
290295300
serilealametleuileglyasnleuasnasphistyrproilepro
305310315320
asnaspleumetaspleuthrthraspleuglnhishisglnalathr
325330335
sersermetthrprogluasphisalatyrvalglyserseraspasp
340345350
glnvalserpheasnasppheglutrptrp
355360
- 还没有人留言评论。精彩留言会获得点赞!