用于多基因联合检测妇科肿瘤的引物组、试剂盒、文库及应用的制作方法
本发明涉及生化检测领域,具体涉及一种用于多基因联合检测妇科肿瘤的引物组、试剂盒、文库及应用。
背景技术:
中国女性生殖道恶性肿瘤发病率居于女性恶性肿瘤的首位,是妇癌患者死亡的主要原因之一,造成妇癌患者死亡率居高不下的主要原因是缺乏早期筛查方法,尤其是卵巢癌。因此,寻求一种早期、简便、特异、无创的筛查方法是改善妇科恶性肿瘤患者预后的亟待解决的重要问题。
早期筛查方法的建立可使妇癌患者得以早发现、早诊断、早治疗,使患者生存率提高、死亡率降低,从而达到推动女性生殖道恶性肿瘤预防控制的目标。此外,特异性基因筛查也可作为治疗后的监测指标预测恶性肿瘤的复发,为判断预后及制定个性化治疗方案提供理论依据。
高通量基因组技术(如微阵列,二代测序技术)的发展为我们实现这个目标提供可能。2012年美国癌症和肿瘤基因图谱(tcga)显示了卵巢癌全基因图谱,发现卵巢癌普遍存在高比率的p53、pi3k、kras和b-raf突变。对子宫内膜癌的基因分析也有类似的发现。这些癌症的共同遗传特征提供了一个对宫颈癌、子宫内膜癌和卵巢癌进行早期癌症诊断的机会。根据已发表的子宫内膜癌和卵巢癌的数据,大约12~14个基因可以代表这两种癌症共有致癌基因,包括:apc、akt1、braf、brca1、brca2、ctnnb1、egfr、fbxw7、kras、nras、pik3ca、ppp2r1a、pten、tp53。与常规液基细胞学异常细胞相比,这些致癌基因突变是肿瘤克隆的特异性标志物,并且在非肿瘤正常细胞中缺乏,而且现有的分子生物学方法可以对宫颈细胞标本中癌细胞进行高敏感性和特异性检测。
随着高通量测序技术的日益成熟,基因检测用于精准医疗越来越成为共识,但临床应用要求基因检测周期短、检测成本低和检测准确性高等条件。靶向测序可以解决基因检测周期短(由于只检测目标区域,因此数据分析周期大大缩短)的问题,同时在一定程度上降低测序成本,因此靶向测序是临床应用的一个趋势。靶向测序有两种较为成熟的方法,其一是液相杂交捕获技术,该技术成熟、稳定,但往往建库周期较长(3天左右),需要较多的贵重仪器(例如打断仪器等),建库实验成本难以降低等,因此不利于临床推广;靶向测序另一方法是多重pcr捕获技术,其优点是建库实验快、周期短(1天)、不需要额外的设备及检测成本低的优势,便于在实验室开展。
技术实现要素:
为了克服现有技术的不足和缺点,本发明的首要目的在于提供一种用于多基因联合检测妇科肿瘤的引物组。
本发明的另一目的在于提供一种用于多基因联合检测妇科肿瘤的试剂盒,该试剂盒包括上述用于多基因联合检测妇科肿瘤的引物组。
本发明的再一目的在于提供一种用于多基因联合检测妇科肿瘤的二代测序dna文库。
本发明的第四个目的在于提供上述用于多基因联合检测妇科肿瘤的二代测序dna文库的构建方法。
本发明的第五个目的在于提供上述用于多基因联合检测妇科肿瘤的引物组、试剂盒和二代测序dna文库的应用。
本发明的目的通过下述技术方案实现:
一种用于多基因联合检测妇科肿瘤的引物组,包括akt1基因引物组、apc基因引物组、braf基因引物组、ctnnb1基因引物组、egfr基因引物组、fbxw7基因引物组、kras基因引物组、nras基因引物组、pik3ca基因引物组、ppp2r1a基因引物组、pten基因引物组、tp53基因引物组、brca1基因引物组和brca2基因引物组;
所述的akt1基因引物组包括1对引物,所述的akt1基因引物组的核酸序列如seqidno.1~2所示;
所述的apc基因引物组包括5对引物,所述的apc基因引物组的核酸序列如seqidno.3~12所示;
所述的braf基因引物组基因引物组包括1对引物,所述的braf基因引物组的核酸序列如seqidno.13~14所示;
所述的ctnnb1基因引物组基因引物组包括1对引物,所述的ctnnb1基因引物组的核酸序列如seqidno.15~16所示;
所述的egfr基因引物组包括4对引物,所述的egfr基因引物组的核酸序列如seqidno.17~24所示;
所述的fbxw7基因引物组包括6对引物,所述的fbxw7基因引物组的核酸序列如seqidno.25~36所示;
所述的kras基因引物组包括3对引物,所述的kras基因引物组的核酸序列如seqidno.37~42所示;
所述的nras基因引物组包括2对引物,所述的nras基因引物组的核酸序列如seqidno.43~46所示;
所述的pik3ca基因引物组包括4对引物,所述的pik3ca基因引物组的核酸序列如seqidno.47~54所示;
所述的ppp2r1a基因引物组包括1对引物,所述的ppp2r1a基因引物组的核酸序列如seqidno.55~56所示;
所述的pten基因引物组包括7对引物,所述的pten基因引物组的核酸序列如seqidno.57~70所示;
所述的tp53基因引物组包括11对引物,所述的tp53基因引物组的核酸序列如seqidno.71~92所示;
所述的brca1基因引物组包括1对引物,所述的brca1基因引物组的核酸序列如seqidno.93~94所示;
所述的brca2基因引物组包括1对引物,所述的brca2基因引物组的核酸序列如seqidno.95~96所示;
一种用于多基因联合检测妇科肿瘤的试剂盒,包含上述用于多基因联合检测妇科肿瘤的引物组;
所述的用于多基因联合检测妇科肿瘤的试剂盒,具体包含如下组分:pcr扩增模块和磁珠纯化模块;
所述的pcr扩增模块包含如下组分:2×kapahifihotstartreadymix、2.5umpre-lm-pcrindex、2.5umpre-lm-pcroligope-1.0和上述用于多基因联合检测妇科肿瘤的引物组;
所述的pre-lm-pcrindex的核酸序列如seqidno.97所示;
所述的pre-lm-pcroligope-1.0的核酸序列如seqidno.98所示;
所述的用于多基因联合检测妇科肿瘤的引物组中各引物的浓度优选为4nmol;
所述的磁珠纯化模块包含magneticbeads和ddh2o;
所述的pcr扩增模块优选包含如下组分:
所述的磁珠纯化模块优选包含如下组分:
magneticbeads90μl/样本;
ddh2o100μl/样本;
一种用于多基因联合检测妇科肿瘤的二代测序dna文库,利用上述试剂盒构建得到;
所述的用于多基因联合检测妇科肿瘤的二代测序dna文库的构建方法,包含如下步骤:
(1)以待测样品的基因组dna为模板,利用上述试剂盒配制多重pcr扩增反应体系,进行多重pcr扩增,通过多重pcr对目标基因进行特异性捕获扩增,得到第一轮pcr反应产物;其中,多重pcr扩增反应体系包含如下组分:2×kapahifihotstartreadymix25μl;用于多基因联合检测妇科肿瘤的引物组8μl;浓度为50ng/μl的基因组dna1μl;ddh2o16μl;
(2)以第一轮pcr反应产物为模板,配制第二轮pcr扩增反应体系,进行第二轮pcr扩增,通过第二轮pcr对不同样本加上测序接头和分子标签,以达到区分不同样本的目的,得到第二轮pcr产物;其中,第二轮pcr扩增反应体系包含如下组分:第一轮pcr反应产物1μl;kapahifihotstartreadymix25μl;2.5umpre-lm-pcrindex4μl;2.5μmpre-lm-pcroligope-1.04μl;
ddh2o16μl;
(3)第二轮pcr产物纯化:在步骤(2)制得的第二轮pcr产物中加入90μlmagneticbeads后,室温孵育,使dna与磁珠充分结合;将装有上述混合物的离心管放回到磁力架上直至溶液变澄清,最后用100μlddh2o将pcr产物从磁珠上洗脱下来,得到用于多基因联合检测妇科肿瘤的二代测序dna文库;
步骤(1)中所述的多重pcr扩增的反应程序优选为:预变性,95℃5min;扩增循环,95℃30sec,55℃30sec,68℃60sec,35个循环;孵育,72℃7min;
步骤(2)中所述的第二轮pcr扩增的反应程序优选为:预变性,98℃45sec;扩增循环,98℃15sec,60℃30sec,72℃30sec,35个循环;孵育,72℃1min;
步骤(3)中所述的孵育的条件优选为室温孵育15min;
所述的用于多基因联合检测妇科肿瘤的引物组、试剂盒和二代测序dna文库在制备检测妇科肿瘤产品中的应用;
本发明相对于现有技术具有如下的优点及效果:
(1)本发明提供了一种用于多基因联合检测妇科肿瘤的引物组,该引物组可在同一pcr反应体系中对14个妇科肿瘤致癌目标基因(apc、akt1、braf、ctnnb1、egfr、fbxw7、kras、nras、pik3ca、ppp2r1a、pten、tp53、brca1、brca2)进行特异性扩增。
(2)本发明提供了一种多基因联合检测妇科肿瘤的试剂盒,该试剂盒基于多重pcr靶向捕获技术(图2),可以在8小时内轻松地完成目标序列的富集,获得可以直接上机测序的高质量文库。
(3)利用本发明提供的引物组和试剂盒构建测序文库只需8小时,其中手工操作时间不到2小时,整个流程简捷,易于实验自动化。
(4)利用本发明提供的引物组和试剂盒建构建好的测序文库(图3),结合二代测序技术,可以检测到1%甚至更低频率的变异,同时假阳性率极低。
(5)本发明提供的引物组、试剂盒和二代测序dna文库可应用到妇科肿瘤14个致癌基因的靶向捕获与基因检测。
附图说明
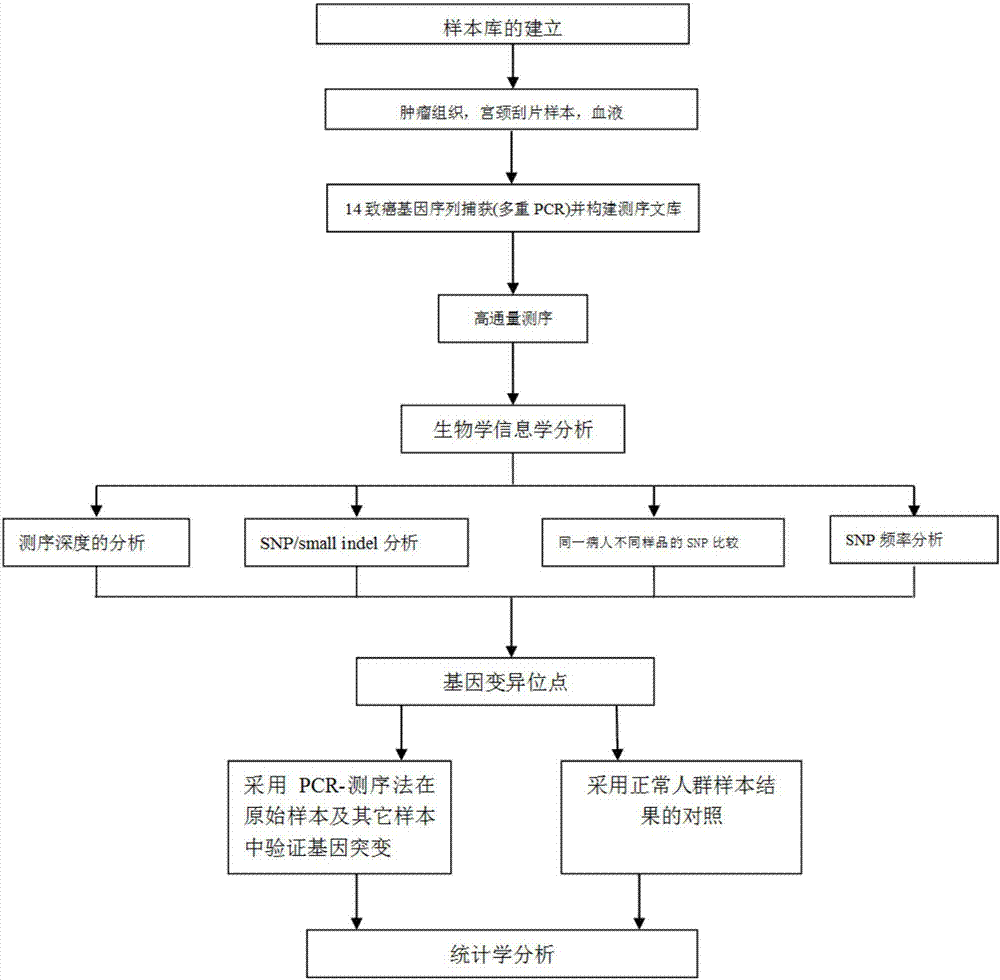
图1是实施例2的技术路线图。
图2是多重pcr扩增示意图。
图3是本发明文库结构示意图。
图4是实施例3brca1基因突变情况分析图。
具体实施方式
下面结合实施例及附图对本发明作进一步详细的描述,但本发明的实施方式不限于此。
实施例中所用的多重pcr+ngs技术包括但不限于illumina的边合成边测序双端测序技术,也可以使iontorrent半导体测序技术,对不同的测序平台只需更改相应的接头序列,目的基因捕获的特异性序列保持不变。以下illumina双端测序方法为例进行阐述。实施例中引物、pre-lm-pcrindex和pre-lm-pcroligope-1.0由上海生工合成。
实施例1
一种用于多基因联合检测妇科肿瘤的试剂盒,具体包含如下组分:pcr扩增模块和磁珠纯化模块;
所述的pcr扩增模块包含如下组分:
所述的磁珠纯化模块包含如下组分:
magneticbeads90μl/样本;
ddh2o100μl/样本。
实施例2
(1)基因组dna提取
采集受检者(受检者是自愿进行高端体检的人)外周血2ml置于edta抗凝管中,超净工作台中取300μledta抗凝血用于基因组dna提取。按照盐析法全血dna提纯试剂盒(厂家:广州美技生物科技有限公司,商品型号:d3311-02)进行基因组dna提取,并用nanodrop测定dna浓度,记录好相应浓度及260/280及260/230的比值。本次测试共对1例样本进行检测。
(2)第一轮多重pcr扩增(实施例1制得的试剂盒pcr扩增模块):以步骤(1)制得的待测样品的基因组dna为模板,利用实施例1制得的试剂盒配制多重pcr扩增反应体系,进行多重pcr扩增(反应程序:95℃5min;95℃30sec,55℃30sec,68℃60sec,35个循环;72℃7min;4℃保持>1h),通过多重pcr对目标基因进行特异性捕获扩增,得到第一轮pcr反应产物(图2);其中,第一轮多重pcr扩增反应体系如表1所示:
表1第一轮多重pcr扩增反应体系
(3)第二轮pcr扩增:以第一轮pcr反应产物为模板,配制第二轮pcr扩增反应体系,进行第二轮pcr扩增(反应程序:98℃45sec;98℃15sec,60℃30sec,72℃30sec,35个循环;72℃1min;4℃保持>1h),通过第二轮pcr对不同样本加上测序接头和分子标签,以达到区分不同样本的目的,得到第二轮pcr产物;其中,第二轮pcr反应体系如表2所示:
表2第二轮pcr反应体系
(4)第二轮pcr产物纯化:加入90μlbeads后,室温孵育15min,使dna与磁珠充分结合;将装有上述混合物的离心管放回到磁力架上直至溶液变澄清,将上清全部转移至一个新的0.5ml离心管中,继续后面的操作;
(5)质检:用qubit染料以及质量分数为1.5%琼脂糖凝胶电泳测定扩增后的dna浓度及片段大小。
(6)文库定量:使用荧光定量pcr对构建好的二代测序文库进行定量。
(7)稀释文库:将构建好的文库稀释至10nm。
(8)上机测序:使用illuminanextseq500二代测序平台对样本进行测序,测序完成后通过对不同样本加的特异标签序列对其进行拆分。
(9)应用生物信息学分析软件nextgene将测序数据转化为fastq文件,并进行数据分析,将测序获得的dna序列片段比对到参考靶基因序列上,对14个致癌基因(akt1、apc、braf、ctnnb1、egfr、fbxw7、kras、nras、pik3ca、pp2r1a、pten、tp53、brca1、brca2)进行snvs和indels的提取,排除基因多态性位点获得靶基因上的突变信息,技术路线如图1所示。
利用实施例1制得的试剂盒构建测序文库只需8小时,其中手工操作时间不到2小时,整个流程简捷,易于实验自动化。本实施例构建好的测序文库(图3),结合二代测序技术,可以检测到1%甚至更低频率的变异,同时假阳性率极低。
实施例3
采集受检者(受检者为自愿进行高端体检的人)外周血2ml提取基因组dna并进行第一轮多重pcr扩增、第二轮pcr扩增、第二轮pcr产物纯化、质检、文库定量、稀释文库、上机测序等;应用生物信息学分析软件nextgene将测序数据转化为fastq文件,并进行数据分析,将测序获得的dna序列片段比对到参考靶基因序列上,对14个致癌基因(akt1、apc、braf、ctnnb1、egfr、fbxw7、kras、nras、pik3ca、pp2r1a、pten、tp53、brca1、brca2)进行snvs和indels的提取,排除基因多态性位点获得靶基因上的突变信息,具体方法参见实施例2。
基因检测结果如图4和表3所示,检测结果质控统计:平均覆盖深度188+/-86x,大于10x覆盖区间占99.8%,大于20x覆盖区间占99.4%检测结论:检测到一个与遗传性乳腺癌/卵巢癌综合征相关的高风险变异。
表3基因检测结果
此基因检测的结果需要医生结合送检者的临床症状及家族史进行解读。我们了解到本送检者目前没有临床表现,为了分析基因检测结果,我们认为所提供信息是准确的。
此次基因检测中,对遗传性肿瘤相关基因进行了检测和分析,检测到brca1基因一个杂合变异c.919delg(p.e307kfs*5)。这个变异在相关临床病例中被报道过,报道的患者为40岁女性临床诊断为遗传性乳腺癌和卵巢癌综合征(pmid:25927356)。这个变异为移码突变,预测可能会导致蛋白质的氨基酸序列提前出现终止密码。该变异所在区域是这个蛋白质的重要组成部分,不同物种的氨基酸序列高度保守。综上所述,依据美国acmgg变异分类指南,此杂合变异为“ii类-可能致病”。
brca1基因相关的疾病为乳腺癌/卵巢癌,遗传方式为常染色体显性遗传。突变携带者在早年患乳腺癌/卵巢癌的风险高于普通人群,乳腺癌的终生患病风险为40~80%,卵巢癌的终生患病风险为11~50%。此外,brca1基因变异也会增加其它肿瘤(前列腺癌、男性乳腺癌和胰腺癌)发生的风险(pmid:20301425)。送检者有罹患此病的可能性,需引起高度注意。
表4扩增引物列表
上述实施例为本发明较佳的实施方式,但本发明的实施方式并不受上述实施例的限制,其他的任何未背离本发明的精神实质与原理下所作的改变、修饰、替代、组合、简化,均应为等效的置换方式,都包含在本发明的保护范围之内。
sequencelisting
<110>张巍
<120>用于多基因联合检测妇科肿瘤的引物组、试剂盒、文库及应用
<130>1
<160>98
<170>patentinversion3.3
<210>1
<211>40
<212>dna
<213>artificial
<220>
<223>引物akt1_for
<400>1
tacacgacgctcttccgatctaccacccgcacgtctgtag40
<210>2
<211>39
<212>dna
<213>artificial
<220>
<223>引物akt1_rev
<400>2
agacgtgtgctcttccgatcagccagtgcttgttgcttg39
<210>3
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-1_for
<400>3
tacacgacgctcttccgatcttgctggatttggttctaggg41
<210>4
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-1_rev
<400>4
agacgtgtgctcttccgatctgccacttgcaaagtttcttc41
<210>5
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-2_for
<400>5
tacacgacgctcttccgatctggaagaacctggaccctctg41
<210>6
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-2_rev
<400>6
agacgtgtgctcttccgatcttttgagagtcgttcgattgc41
<210>7
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-3_for
<400>7
tacacgacgctcttccgatcttgcaacctgttttgtgatgg41
<210>8
<211>42
<212>dna
<213>artificial
<220>
<223>引物apc-3_rev
<400>8
agacgtgtgctcttccgatcaggaaaatgacaatgggaatga42
<210>9
<211>41
<212>dna
<213>artificial
<220>
<223>引物apc-4_for
<400>9
tacacgacgctcttccgatctccactgcatggttcactctg41
<210>10
<211>40
<212>dna
<213>artificial
<220>
<223>引物apc-4_rev
<400>10
agacgtgtgctcttccgatcatcctgtgagcgaagttcca40
<210>11
<211>43
<212>dna
<213>artificial
<220>
<223>引物apc-5_for
<400>11
tacacgacgctcttccgatcttgcctctttctcttggttttca43
<210>12
<211>42
<212>dna
<213>artificial
<220>
<223>引物apc-5_rev
<400>12
agacgtgtgctcttccgatcggacctaagcaagctgcagtaa42
<210>13
<211>46
<212>dna
<213>artificial
<220>
<223>引物braf_for
<400>13
tacacgacgctcttccgatcttcaccacattacatacttaccatgc46
<210>14
<211>42
<212>dna
<213>artificial
<220>
<223>引物braf_rev
<400>14
agacgtgtgctcttccgatcaaggggatctcttcctgtatcc42
<210>15
<211>49
<212>dna
<213>artificial
<220>
<223>引物ctnnb1_for
<400>15
tacacgacgctcttccgatctaaagtaacatttccaatctactaatgct49
<210>16
<211>41
<212>dna
<213>artificial
<220>
<223>引物ctnnb1_rev
<400>16
agacgtgtgctcttccgatctgagaaaatccctgttcccac41
<210>17
<211>41
<212>dna
<213>artificial
<220>
<223>引物egfr-1_for
<400>17
tacacgacgctcttccgatcttggagcctcttacacccagt41
<210>18
<211>42
<212>dna
<213>artificial
<220>
<223>引物egfr-1_rev
<400>18
agacgtgtgctcttccgatcaaaaacactggagtttcccaaa42
<210>19
<211>41
<212>dna
<213>artificial
<220>
<223>引物egfr-2_for
<400>19
tacacgacgctcttccgatcttctggatcccagaaggtgag41
<210>20
<211>40
<212>dna
<213>artificial
<220>
<223>引物egfr-2_rev
<400>20
agacgtgtgctcttccgatcggccagtgctgtctctaagg40
<210>21
<211>40
<212>dna
<213>artificial
<220>
<223>引物egfr-3_for
<400>21
tacacgacgctcttccgatctcacactgacgtgcctctcc40
<210>22
<211>40
<212>dna
<213>artificial
<220>
<223>引物egfr-3_rev
<400>22
agacgtgtgctcttccgatcttatctcccctccccgtatc40
<210>23
<211>42
<212>dna
<213>artificial
<220>
<223>引物egfr-4_for
<400>23
tacacgacgctcttccgatctttcagggcatgaactacttgg42
<210>24
<211>40
<212>dna
<213>artificial
<220>
<223>引物egfr-4_rev
<400>24
agacgtgtgctcttccgatcatcctcccctgcatgtgtta40
<210>25
<211>45
<212>dna
<213>artificial
<220>
<223>引物fbxw7-1_for
<400>25
tacacgacgctcttccgatcttgattcatcaggagagcatttaag45
<210>26
<211>43
<212>dna
<213>artificial
<220>
<223>引物fbxw7-1_rev
<400>26
agacgtgtgctcttccgatcttgtttttctgtttctccctctg43
<210>27
<211>43
<212>dna
<213>artificial
<220>
<223>引物fbxw7-2_for
<400>27
tacacgacgctcttccgatctgatggtatccatgtggtgagtg43
<210>28
<211>41
<212>dna
<213>artificial
<220>
<223>引物fbxw7-2_rev
<400>28
agacgtgtgctcttccgatctttgtgatgctaaggctccat41
<210>29
<211>46
<212>dna
<213>artificial
<220>
<223>引物fbxw7-3_for
<400>29
tacacgacgctcttccgatctacacccaatgaagaatgtaattgat46
<210>30
<211>45
<212>dna
<213>artificial
<220>
<223>引物fbxw7-3_rev
<400>30
agacgtgtgctcttccgatcggttgtgtgtagatgtgagttttcc45
<210>31
<211>45
<212>dna
<213>artificial
<220>
<223>引物fbxw7-4_for
<400>31
tacacgacgctcttccgatctttctgttacattgtgcagagttca45
<210>32
<211>41
<212>dna
<213>artificial
<220>
<223>引物fbxw7-4_rev
<400>32
agacgtgtgctcttccgatctggttttgagcagagagatgg41
<210>33
<211>41
<212>dna
<213>artificial
<220>
<223>引物fbxw7-5_for
<400>33
tacacgacgctcttccgatctggaagaagtcccaaccatga41
<210>34
<211>44
<212>dna
<213>artificial
<220>
<223>引物fbxw7-5_rev
<400>34
agacgtgtgctcttccgatctcacttttcctttctacccaaaag44
<210>35
<211>42
<212>dna
<213>artificial
<220>
<223>引物fbxw7-6_for
<400>35
tacacgacgctcttccgatctgaatctgcattcccagagaca42
<210>36
<211>40
<212>dna
<213>artificial
<220>
<223>引物fbxw7-6_rev
<400>36
agacgtgtgctcttccgatccctgtttcccatcctcttcc40
<210>37
<211>46
<212>dna
<213>artificial
<220>
<223>引物kras-1_for
<400>37
tacacgacgctcttccgatctgtccacaaaatgattctgaattagc46
<210>38
<211>42
<212>dna
<213>artificial
<220>
<223>引物kras-1_rev
<400>38
agacgtgtgctcttccgatcacgatacacgtctgcagtcaac42
<210>39
<211>42
<212>dna
<213>artificial
<220>
<223>引物kras-2_for
<400>39
tacacgacgctcttccgatcttccctcattgcactgtactcc42
<210>40
<211>40
<212>dna
<213>artificial
<220>
<223>引物kras-2_rev
<400>40
agacgtgtgctcttccgatcggtgcttagtggccatttgt40
<210>41
<211>42
<212>dna
<213>artificial
<220>
<223>引物kras-3_for
<400>41
tacacgacgctcttccgatctgacacaaaacaggctcaggac42
<210>42
<211>40
<212>dna
<213>artificial
<220>
<223>引物kras-3_rev
<400>42
agacgtgtgctcttccgatcagaaaccaaagccaaaagca40
<210>43
<211>41
<212>dna
<213>artificial
<220>
<223>引物nras-1_for
<400>43
tacacgacgctcttccgatctgattgtcagtgcgcttttcc41
<210>44
<211>40
<212>dna
<213>artificial
<220>
<223>引物nras-1_rev
<400>44
agacgtgtgctcttccgatcgctaaggatgggggttgcta40
<210>45
<211>43
<212>dna
<213>artificial
<220>
<223>引物nras-2_for
<400>45
tacacgacgctcttccgatcttggtctctcatggcactgtact43
<210>46
<211>43
<212>dna
<213>artificial
<220>
<223>引物nras-2_rev
<400>46
agacgtgtgctcttccgatcattagcaatttgagggacaaacc43
<210>47
<211>41
<212>dna
<213>artificial
<220>
<223>引物pik3ca-1_for
<400>47
tacacgacgctcttccgatctgaaaaagccgaaggtcacaa41
<210>48
<211>40
<212>dna
<213>artificial
<220>
<223>引物pik3ca-1_rev
<400>48
agacgtgtgctcttccgatcatgcccccaagaatcctagt40
<210>49
<211>48
<212>dna
<213>artificial
<220>
<223>引物pik3ca-2_for
<400>49
tacacgacgctcttccgatctacagaaatattttagaaagggacaaca48
<210>50
<211>42
<212>dna
<213>artificial
<220>
<223>引物pik3ca-2_rev
<400>50
agacgtgtgctcttccgatcagaaaataccccctccatcaac42
<210>51
<211>46
<212>dna
<213>artificial
<220>
<223>引物pik3ca-3_for
<400>51
tacacgacgctcttccgatctgatccaatccatttttgttgtccag46
<210>52
<211>44
<212>dna
<213>artificial
<220>
<223>引物pik3ca-3_rev
<400>52
agacgtgtgctcttccgatctccaaactgaccaaactgttctta44
<210>53
<211>47
<212>dna
<213>artificial
<220>
<223>引物pik3ca-4_for
<400>53
tacacgacgctcttccgatcttgactttaccttatcaatgtctcgaa47
<210>54
<211>39
<212>dna
<213>artificial
<220>
<223>引物pik3ca-4_rev
<400>54
agacgtgtgctcttccgatcgctcgcccccttaatctct39
<210>55
<211>41
<212>dna
<213>artificial
<220>
<223>引物ppp2r1a_for
<400>55
tacacgacgctcttccgatctggtacttccggaacctgtgc41
<210>56
<211>40
<212>dna
<213>artificial
<220>
<223>引物ppp2r1a_rev
<400>56
agacgtgtgctcttccgatcccgagtcctagggagaggag40
<210>57
<211>41
<212>dna
<213>artificial
<220>
<223>引物pten-1_for
<400>57
tacacgacgctcttccgatctcatccgtctactcccacgtt41
<210>58
<211>39
<212>dna
<213>artificial
<220>
<223>引物pten-1_rev
<400>58
agacgtgtgctcttccgatcatcagctaccgccaagtcc39
<210>59
<211>41
<212>dna
<213>artificial
<220>
<223>引物pten-2_for
<400>59
tacacgacgctcttccgatctttcgtccctttccagcttta41
<210>60
<211>47
<212>dna
<213>artificial
<220>
<223>引物pten-2_rev
<400>60
agacgtgtgctcttccgatcggaatccagtgtttcttttaaatacct47
<210>61
<211>43
<212>dna
<213>artificial
<220>
<223>引物pten-3_for
<400>61
tacacgacgctcttccgatctgaaacccaaaatctgttttcca43
<210>62
<211>41
<212>dna
<213>artificial
<220>
<223>引物pten-3_rev
<400>62
agacgtgtgctcttccgatcgaccataacccaccacagcta41
<210>63
<211>44
<212>dna
<213>artificial
<220>
<223>引物pten-4_for
<400>63
tacacgacgctcttccgatctttgttaatggtggctttttgttt44
<210>64
<211>45
<212>dna
<213>artificial
<220>
<223>引物pten-4_rev
<400>64
agacgtgtgctcttccgatcaaatgatctaacaatgctcttggac45
<210>65
<211>44
<212>dna
<213>artificial
<220>
<223>引物pten-5_for
<400>65
tacacgacgctcttccgatctcatggaaggatgagaatttcaag44
<210>66
<211>40
<212>dna
<213>artificial
<220>
<223>引物pten-5_rev
<400>66
agacgtgtgctcttccgatctggctacgacccagttacca40
<210>67
<211>48
<212>dna
<213>artificial
<220>
<223>引物pten-6_for
<400>67
tacacgacgctcttccgatcttgtatctcactcgataatctggatgac48
<210>68
<211>46
<212>dna
<213>artificial
<220>
<223>引物pten-6_rev
<400>68
agacgtgtgctcttccgatctgtcacattataaagattcaggcaat46
<210>69
<211>45
<212>dna
<213>artificial
<220>
<223>引物pten-7_for
<400>69
tacacgacgctcttccgatctagtttgacagttaaaggcatttcc45
<210>70
<211>45
<212>dna
<213>artificial
<220>
<223>引物pten-7_rev
<400>70
agacgtgtgctcttccgatctgtccttattttggatatttctccc45
<210>71
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-1_for
<400>71
tacacgacgctcttccgatctaccagccctgtcgtctctc40
<210>72
<211>42
<212>dna
<213>artificial
<220>
<223>引物tp53-1_rev
<400>72
agacgtgtgctcttccgatcgccctgactttcaactctgtct42
<210>73
<211>45
<212>dna
<213>artificial
<220>
<223>引物tp53-2_for
<400>73
tacacgacgctcttccgatctgcctcagattcacttttatcacct45
<210>74
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-2_rev
<400>74
agacgtgtgctcttccgatcaccaggagccattgtctttg40
<210>75
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-3_for
<400>75
tacacgacgctcttccgatctctcctcccagagaccccagt41
<210>76
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-3_rev
<400>76
agacgtgtgctcttccgatccatgagcgctgctcagatag40
<210>77
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-4_for
<400>77
tacacgacgctcttccgatctcctaggaaggcaggggagt40
<210>78
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-4_rev
<400>78
agacgtgtgctcttccgatctgcatgttgcttttgtaccg40
<210>79
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-5_for
<400>79
tacacgacgctcttccgatctaaaccgtagctgccctggta41
<210>80
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-5_rev
<400>80
agacgtgtgctcttccgatctgactgctcttttcacccatc41
<210>81
<211>42
<212>dna
<213>artificial
<220>
<223>引物tp53-6_for
<400>81
tacacgacgctcttccgatcttcatcttgggcctgtgttatc42
<210>82
<211>44
<212>dna
<213>artificial
<220>
<223>引物tp53-6_rev
<400>82
agacgtgtgctcttccgatcgatgagaggtggatgggtagtagt44
<210>83
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-7_for
<400>83
tacacgacgctcttccgatctgaagacccaggtccagatga41
<210>84
<211>39
<212>dna
<213>artificial
<220>
<223>引物tp53-7_rev
<400>84
agacgtgtgctcttccgatcagaaatgcagggggatacg39
<210>85
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-8_for
<400>85
tacacgacgctcttccgatctgaggcataactgcacccttg41
<210>86
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-8_rev
<400>86
agacgtgtgctcttccgatcgggagtagatggagcctggt40
<210>87
<211>39
<212>dna
<213>artificial
<220>
<223>引物tp53-9_for
<400>87
tacacgacgctcttccgatctactgccttccgggtcact39
<210>88
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-9_rev
<400>88
agacgtgtgctcttccgatcagcccaacccttgtccttac40
<210>89
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-10_for
<400>89
tacacgacgctcttccgatctgaggctgtcagtggggaac40
<210>90
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-10_rev
<400>90
agacgtgtgctcttccgatcaacatatttgcatggggtgtg41
<210>91
<211>41
<212>dna
<213>artificial
<220>
<223>引物tp53-11_for
<400>91
tacacgacgctcttccgatctccatgggactgactttctgc41
<210>92
<211>40
<212>dna
<213>artificial
<220>
<223>引物tp53-11_rev
<400>92
agacgtgtgctcttccgatctcatctggacctgggtcttc40
<210>93
<211>46
<212>dna
<213>artificial
<220>
<223>引物brca1-for
<400>93
tacacgacgctcttccgatctgcagcgtttatagtctgcttttaca46
<210>94
<211>45
<212>dna
<213>artificial
<220>
<223>引物brca1-rev
<400>94
agacgtgtgctcttccgatcctactgaatgcaaaggacaccacac45
<210>95
<211>49
<212>dna
<213>artificial
<220>
<223>引物brca2-for
<400>95
tacacgacgctcttccgatctgatattatttgccttaaaaacatatatg49
<210>96
<211>48
<212>dna
<213>artificial
<220>
<223>引物brca2-rev
<400>96
agacgtgtgctcttccgatcgagggagaacagatataaataaaaagct48
<210>97
<211>58
<212>dna
<213>artificial
<220>
<223>引物pre-lm-pcroligope-1.0
<220>
<221>硫代磷酸化修饰
<222>(58)..(58)
<400>97
aatgatacggcgaccaccgagatctacactctttccctacacgacgctcttccgatct58
<210>98
<211>58
<212>dna
<213>artificial
<220>
<223>引物pre-lm-pcrindex
<220>
<221>8个随机碱基
<222>(24)..(25)
<220>
<221>硫代磷酸化修饰
<222>(58)..(58)
<400>98
caagcagaagacggcatacgagatgtgactggagttcagacgtgtgctcttccgatct58
- 还没有人留言评论。精彩留言会获得点赞!
- 玉米低镁条件下特异性转运镁离子基因ZmMGT10及其应用的制造方法与工艺
- CRISPR‑Cas9特异性敲除猪SLA‑3基因的方法及用于特异性靶向SLA‑3基因的sgRNA与制造工艺
- 毛酸浆的分子特异性标记引物及鉴别方法与制造工艺
- 一种检测CYP2C9基因多态性的ARMS引物的制造方法与工艺
- 构建在海马体区域特异性敲除IKKα基因的小鼠模型的方法及打靶载体和试剂盒与制造工艺
- 使用重叠非等位基因特异性引物和等位基因特异性阻断剂寡核苷酸的组合物进行等位基因特异性扩增的制造方法与工艺
- 一种利用线粒体D-loop区特异区域鉴定鼋的标记引物及方法
- 一种用于检测大豆拟茎点种腐病菌的特异性lamp引物组合物及其应用
- 一种针对膨胀污泥中Eikelboom Type 0092型丝状菌群特异性引物和方法
- 脯氨酸特异性蛋白酶基因及其应用