一种酶法合成3‑O‑葡萄糖基甘草次酸的方法与流程
技术领域:
本发明涉及一种合成3-o-葡萄糖基甘草次酸的方法,属于生物工程与技术领域。
背景技术:
:
甘草次酸属于五环三萜类齐墩果烷型天然产物,主要来源于植物甘草的根茎。甘草次酸具有多种药理和生物活性,所以被广泛应用于医药领域。在临床医药领域因其具有抗肿瘤、抗炎,抗病毒、抗溃疡、抗过敏、抗氧化和肾上腺皮质激素样等多种药理作用而被广泛应用。甘草次酸还能够与肝细胞结合抑制肝脏细胞凋亡和细胞坏死。但是,甘草次酸因其结构特点在临床应用时常会遇到类醛固酮增多症,水溶性差,生物利用度低等问题。因此,研究人员一直致力于以甘草次酸为前体物,对其进行一定的结构修饰来改善这些缺点,从而获得更加低毒、稳定、高效的新型药物目标分子或新功能新化合物。
目前,人们对甘草次酸的结构改造主要集中在甘草次酸的碳3位的羟基,碳11位的酮基和碳30位的羧基等位置。修饰的方式主要有改变甘草次酸的某些官能团,与金属化合物或小分子化合物作用,引入金属离子或小分子化合物修饰甘草次酸。甘草次酸衍生物主要包括甘草次酸盐类,甘草次酸酯类,甘草次酸酰胺类和甘草次酸其他类衍生物。
糖基化修饰作为一种重要的修饰反应不仅广泛存在天然产物合成的过程,而且在天然先导化合物改性方面也有着重要应用。亲水性的糖类结合到糖苷配基上可以提高与作用位点结合的特异性来改变母药物的药理活性。改善化合物的水溶性,稳定性、分泌性、减小糖苷配基毒副作用和调节血浆半衰期。在对甘草次酸的糖基化研究中,现有的方法是先对甘草次酸和糖基先进行基团保护修饰,再通过有机合成方法合成含有糖配基的甘草次酸糖基衍生物。在此过程中,反应步骤繁琐,反应条件苛刻,耗费时间长且降低产率,反应时常需要大量用有毒有害溶剂,造成环境污染。酶法合成甘草次酸糖基衍生物能有效避免传统有机合成方法的缺点,酶催化效率高,反应步骤少提高产率,且环境友好,在温和反应条件下,直接将糖基供体中的糖基转移连接到甘草次酸分子上,容易分离甘草次酸糖基化产物。
技术实现要素:
:
本发明的目的是提供一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene14953的基因。
本发明的第二个目的是提供一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene14953的基因编码的蛋白质。
本发明的第三个目的是提供一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene20323的基因。
本发明的第四个目的是提供一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene20323的基因编码的蛋白质。
本发明的第五个目的是提供一种合成3-o-葡萄糖基甘草次酸的方法,通过异源表达制备得到的糖基转移酶unigene14953,和/或unigene20323,和/或ugt73c11,和/或ugt73c5,和/或ugt73c6来催化合成3-o-葡萄糖基甘草次酸,开辟了一条以尿苷二磷酸葡萄糖为糖基供体合成3-o-葡萄糖基甘草次酸,为甘草次酸的修饰和3-o-葡萄糖基甘草次酸的合成提供途径和方法。
本发明的技术方案如下:
一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene14953的基因,它是序列表中seqidno.1所述的核苷酸序列。
一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene14953的基因编码的蛋白质,它是序列表中seqidno.2所述的氨基酸序列。
一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene20323的基因,它是序列表中seqidno.3所述的核苷酸序列。
一种催化甘草次酸进行糖基转移反应的糖基转移酶unigene20323的基因编码的蛋白质,它是序列表中seqidno.4所述的氨基酸序列。
一种合成3-o-葡萄糖基甘草次酸的方法,包括以下步骤:
1、构建糖基转移酶基因工程菌生产糖基转移酶unigene14953,或unigene20323,或ugt73c11,或ugt73c5,或ugt73c6;
2、以获得的糖基转移酶unigene14953,或unigene20323,或ugt73c11,或ugt73c5,或ugt73c6粗酶液或浓缩酶液为催化剂,以甘草次酸和尿苷二磷酸葡萄糖为底物合成3-o-葡萄糖基甘草次酸。
在实际实施过程中,上述1步骤包含如下具体工艺:a构建生产糖基转移酶unigene14953,或unigene20323,或ugt73c11,或ugt73c5,或ugt73c6的基因工程菌;b基因工程菌生产糖基转移酶unigene14953,或unigene20323,或ugt73c11,或ugt73c5,或ugt73c6。
所述a构建生产糖基转移酶基因工程菌,可采用任何现有已知的表达载体和其相应表达宿主菌,按照常规的转化步骤或商品宿主菌的使用说明进行操作,构建含有所述的糖基转移酶体基因工程菌。本发明的一些实施例优选采用大肠杆菌作为表达宿主。包括以下步骤:
(1)通过化学合成或从植物cdna中克隆得到糖基转移酶基因unigene14953、unigene20323、ugt73c11、ugt73c5和ugt73c6;该基因的核苷酸序列如seqidno.1、seqidno.3、seqidno.8、seqidno.9和seqidno.10;
(2)将(1)克隆得到的糖基转移酶基因分别大肠杆菌表达质粒pet28a相连接,获得重组质粒。
(3)用(2)重组质粒pet28a转化大肠杆菌e.colibl21(de3)感受态细胞。
(5)筛选得到大肠杆菌工程菌e.colibl21(de3)/pet28a-ugt73c11、e.colibl21(de3)/pet28a-ugt73c5、e.colibl21(de3)/pet28a-ugt73c6、e.colibl21(de3)/pet28a-unigene14953和e.colibl21(de3)/pet28a-unigene20323。
所述b发酵基因工程菌生产糖基转移酶unigene14953、unigene20323、ugt73c11、ugt73c5和ugt73c6,包括以下步骤:将大肠杆菌基因工程菌进行发酵,发酵结束后,将诱导的大肠杆菌基因工程菌破碎收集上清液,即为含有糖基转移酶的粗酶液。
在实际实施过程中,上述2步骤包含如下具体工艺:在反应容器中分别添加甘草次酸和尿苷二磷酸葡萄糖,加入发酵所得含有糖基转移酶的粗酶液进行反应。
所述反应在ph5.0~11.0、25~55℃下反应2h。
所述反应产物通过hplc检测。
采用本发明具有催化效率高,反应条件温和,高效,绿色安全等优点。
附图说明:
图1本发明实施例4中糖基转移酶催化产生3-o-葡萄糖基甘草次酸高效液相色谱图
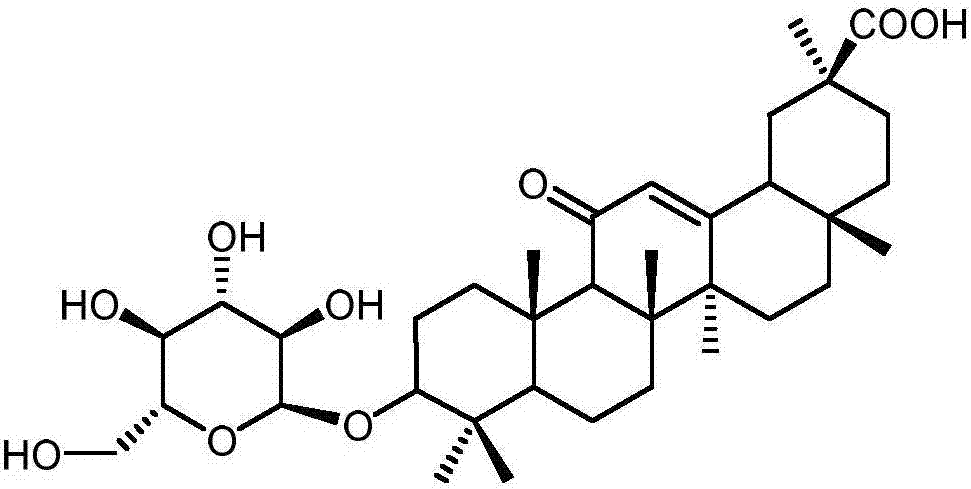
图2本发明实施例4中产物3-o-葡萄糖基甘草次酸分子式。
图3本发明实施例6中糖基转移酶催化产生3-o-葡萄糖基甘草次酸质谱图
图4本发明实施例6中甘草次酸与糖基转移酶催化产生3-o-葡萄糖基甘草次酸红外波谱图
图5本发明实施例7中糖基转移酶在ph5.0-11.0的相对活性。
图6本发明实施例8中糖基转移酶在25-55℃的相对活性。
具体实施方式:
下面结合实施例,对本发明的具体实施方式进一步详细描述。以下实施例用于说明本发明,但不用来限制本发明的范围。
实验例1:合成3-o-葡萄糖基甘草次酸糖基转移酶基因的获得
a:糖基转移酶unigene14953和unigene20323基因的获得
根据甘草转录组数据库筛选,得到糖基转移酶基因unigene14953和unigene20323,设计引物:
53-f:5’>atggacgttgctgaagaacagcc<3’(如seqidno.11所示);
53-r:5’>ttagttaagctgcttagagtctctc<3’(如seqidno.12所示);
23-f:5’>atggttttccaagcaaaccaacc<3’(如seqidno.13所示);
23-r:5’>agtttcaactttactacttgattgt<3’(如seqidno.14所示);
以乌拉尔甘草cdna为模版,使用extaq酶进行pcr扩增,分别得到1434bp片段的unigene14953基因和1470bp片段的unigene20323基因,以seqidno.1和seqidno.3所示,克隆至pmd19-t载体,测序确定糖基转移酶基因unigene14953和unigene20323完整序列。seqidno.1所示片段表达的氨基酸序列用seqidno.2所示,seqidno3所示片段表达的氨基酸序列用seqidno.4所示。
b:糖基转移酶ugt73c11基因的获得
根据糖基转移酶ugt73c11基因(genbank注册序列号为afn26664.1)序列,通过密码子优化,化学合成后优化后的糖基转移酶ugt73c11基因片段,如seqidno.8所示。seqidno.8所示片段表达的氨基酸序列用seqidno.5所示。
c:糖基转移酶ugt73c5和ugt73c6基因的获得
根据糖基转移酶ugt73c5基因(genbank注册序列号为np_181218.1)序列和糖基转移酶ugt73c6基因(genbank注册序列号为oap07438.1)序列,设计引物:
c5-f:5’>atggtttccgaaacaaccaaatcttctcca<3’(如seqidno.15所示);
c5-r:5’>tcaattattgggttctgccagttccatt<3’(如seqidno.16所示);
c6-f:5’>atggctttcgaaaaaaacaacgaacctttt<3’(如seqidno.17所示);
c6-r:5’>tcaattattggactgtgctagttgcattat<3’(如seqidno.18所示);
以拟南芥cdna为模版,使用extaq酶进行pcr扩增,分别得到1488bp片段的ugt73c5基因和1488bp片段的ugt73c6基因,以seqidno.9和seqidno.10所示,克隆至pmd19-t载体,测序确定糖基转移酶基因ugt73c5和ugt73c6完整序列。seqidno.9所示片段表达的氨基酸序列用seqidno.6所示,seqidno10所示片段表达的氨基酸序列用seqidno.7所示。
实施例2:构建含有糖基转移酶的大肠杆菌工程菌
构建含有糖基转移酶ugt73c11基因的大肠杆菌工程菌e.colibl21(de3)/pet28a-ugt73c11,化学合成糖基转移酶ugt73c11基因片段(seqidno.8所示)为模板,设计上下游引物并加入酶切位点ecorⅰ、salⅰ和保护碱基:
e-c11-f:5’>ccggaattcatggtttctgaaatcacccacaaat<3’(如seqidno.19所示);带有ecorⅰ的酶切位点。
e-c11-r:5’>acgcgtcgacgttgttagactgagccagctgcatgat<3’(如seqidno.20所示);带有salⅰ的酶切位点。
pcr反应体系为:模板1μl,上下游引物各2μl,primerstarmix(宝生物公司)25μl,用双蒸水不足50μl。pcr反应条件:预变性98℃1min,变性98℃10s、退火58℃5s、延伸72℃1min30s,循环30次,72℃10min,4℃保存。
将克隆得到的ugt73c11基因进行胶回收。回收后的ugt73c11基因和原核表达载体pet28a。分别用限制性内切酶ecorⅰ和salⅰ进行双酶切,酶切体系:ecorⅰ2μl和salⅰ2μl,10xdigestbuffer5μl,dna片段30μl,用双蒸水补足50μl的酶切体系,酶切条件为37℃、2h。酶切后回收酶切产物。
将酶切回收后的ugt73c11片段和载体pet28a用t4dna连接酶进行连接,连接体系ugt73c117μl,载体pet28a1μl,10xligasebuffer1μl,t4dnaligase1μl。反应条件为16℃过夜连接。将连接产物转化大肠杆菌bl21(de3)感受态细胞,涂布于含有100mg/l卡那霉素的固体lb培养基(蛋白胨10g/l,酵母提取物5g/l,氯化钠10g/l,20g/l琼脂糖)平板上,37℃培养。
采用菌落pcr和测序方法鉴定转化子。菌落pcr体系:模板lb平板单菌落,ugt73c11上下游引物各1μl,2xrtaqmix(宝生物公司)10μl,用双蒸水补足20μl.pcr条件:预变性94℃5min,变性94℃30s、退火58℃30s、延伸72℃1min30s,循环30次,72℃10min,4℃保存。经菌落pcr验证含有目标条带的转化子送dna测序,确定大肠杆菌工程菌e.colibl21(de3)/pet28a-ugt73c11构建成功。
用同样的方法分别构建含有糖基转移酶基因unigene14953、unigene20323、ugt73c5和ugt73c6的大肠杆菌工程菌e.colibl21(de3)/pet28a-unigene14953、e.colibl21(de3)/pet28a-unigene20323、e.colibl21(de3)/pet28a-ugt73c5和e.colibl21(de3)/pet28a-ugt73c6。
所用引物为:
e-c5-f:5’>cgcggatccatggtttccgaaacaaccaaatcttctcca<3’(如seqidno.21所示);带有bamhⅰ的酶切位点。
e-c5-r:上游引物::5’>cgcggatccattattgggttctgccagttccatt<3’(如seqidno.22所示);带有bamhⅰ的酶切位点。
e-c6-f:5’>cgcggatccatggctttcgaaaaaaacaacgaacctttt<3’(如seqidno.23所示);带有bamhⅰ的酶切位点。
e-c6-r:5’>acgcgtcgacattattggactgtgctagttgcattat<3’(如seqidno.24所示);带有salⅰ的酶切位点。
e-53-f:5’>cgcggatccatggacgttgctgaagaacagcc<3’(如seqidno.25所示);带有bamhⅰ的酶切位点。
e-53-r:5’>acgcgtcgacgttaagctgcttagagtctctc<3’(如seqidno.26所示);带有salⅰ的酶切位点。
e-23-f:5’>cgcggatccatggttttccaagcaaaccaacc<3’(如seqidno.27所示);带有bamhⅰ的酶切位点。
e-23-r:5’>acgcgtcgacagtttcaactttactacttgattgt<3’(如seqidno.28所示);带有salⅰ的酶切位点。
实施例3:大肠杆菌基因工程菌的发酵
(1)挑取鉴定正确的大肠杆菌工程菌接种于含有100mg/l卡那霉素的lb液体培养基(蛋白胨10g/l,酵母提取物5g/l,氯化钠10g/l)中过夜培养,培养条件37℃,170rpm。
(2)取过夜培养的菌液3ml接种于300ml含有100mg/l卡那霉素的lb液体培养基中培养3-5h至od600=0.6,培养条件37℃,170rpm。
(3)加入诱导剂iptg,使其终浓度为0.5mm/l,继续培养,培养条件变为16℃,170rpm,8-10h。
(4)将获得的发酵液室温,8000g离心10min后,收集菌体。
(5)25ml的50mm的ph7.0的pbs缓冲液重悬菌体,低温高压破碎机用裂解菌体。
(6)将裂解的菌体在4℃,12000g离心10min,弃沉淀,收集上清,获得含有糖基转移酶的混合液。
实施例4:糖基转移酶催化合成3-o-葡萄糖基甘草次酸
将大肠杆菌工程菌获得的含有糖基转移酶unigene14953、unigene20323、ugt73c11、ugt73c5和ugt73c6粗酶液中分别加入0.1μm甘草次酸,0.1μm尿苷二磷酸葡萄糖进行反应,反应条件37℃,2h。
hplc检测3-o-葡萄糖基甘草次酸产物。取反应物100μl加入900μl的甲醇12000rpm离心10min,取上清液适度稀释后用0.22μm超滤膜过滤,并进行hplc分析。色谱条件如下:岛津hplc色谱仪,岛津自动进样器,液相色谱柱为反向c18硅胶柱(4.6mm×250mm),lc-10a紫外检测器,检测波长为254nm;流动相为冰醋酸水溶液和甲醇双相(v/v=16:84)等梯度洗脱,流速1(mlmin-1);柱温40℃。经过糖基转移酶ugt73c11、ugt73c5、ugt73c6、unigene14953和unigene20323催化后均能检测如图1所示色谱图,其中箭头所指峰为3-o-葡萄糖基甘草次酸分子式见图2。结果说明糖基转移酶ugt73c11、ugt73c5、ugt73c6、unigene14953和unigene20323催化合成3-o-葡萄糖基甘草次酸。
实施例5:3-o-葡萄糖基甘草次酸的分离纯化
1.将糖基转移酶催化反应混合液15000rpm离心10min,分离上清和沉淀,将沉淀用甲醇重悬涡旋振荡5min。
2.将1得到的混合液15000rpm离心10min,分离收集上清。
3.将2得到的上清旋转蒸发浓缩。
4.将3得到的浓缩液用半制备液相分离纯化产物。条件如下:
流动相a为甲醇,流动相b为0.6%冰醋酸水溶液,梯度洗脱。流动相a80%,流动相b20%,流速5ml/min。柱子,岛津c18反向色谱柱,10×25cm,60min。
5.将纯化出的产物,通过旋转蒸发仪和真空冷冻干燥仪进行浓缩干燥,得到白色粉末。
实施例6:3-o-葡萄糖基甘草次酸的鉴定
1.取1mg实施例5中纯化产物产物溶于200μl甲醇进行质谱分析。图3为3-o-葡萄糖基甘草次酸产物的质谱图。结果表明产物的分子量为632,说明产物为甘草次酸连接了一个葡萄糖分子。
2.取1mg实施例5中纯化产物和1mg底物甘草次酸分别与200mg纯kbr研细均匀,置于模具中,用(5-10)x107pa压力在油压机上压成透明薄片,进行红外光谱检测。图4为反应产物与甘草次酸的红外分析图。由图可知产物与甘草次酸的红外光谱相比,羧基(-cooh)还存在纯化的产物中,特征峰在2800-3100cm-1之间。说明糖基没有连接到甘草次酸c30位的羧基上。但在1050-1150cm-1有明显的新峰出现,应该是因为葡萄糖基连接到甘草次酸后,由葡糖糖上的羟基引起的。综上所述,甘草次酸的糖基化产物应该是3-o-葡萄糖基甘草次酸。
3.取5mg纯化产物与5mg甘草次酸,用氘代甲醇溶解,进行1h谱分析。表1为纯化产物与甘草次酸的h谱数据。h谱数据表明葡萄糖分子连接到甘草次酸分子上,并且葡萄糖分子与甘草次酸是通过β糖苷键的方式连接。
表1:甘草次酸和单葡萄糖甘草次酸1hnmr数据
实施例7:酶催化反应的最适ph
将适度稀释糖基转移酶ugt73c11、ugt73c5、ugt73c6、unigene14953和unigene20323的粗酶液置于不同ph缓冲液中:磷酸钾缓冲液,50mm、ph5.0-7.0;tris-hcl缓冲液,50mm、ph8.0-8.9;nahco3-naoh缓冲液,50mmm、ph10.0-11.0。各取100μl不同ph的粗酶液,加入0.1μm甘草次酸和0.1μm尿苷二磷酸葡萄糖,37℃,反应2h后进行酶活测定,研究糖基转移酶的最适ph。由图5可知,重组酶在ph为5.0-11.0之间均能合成3-o-葡萄糖基甘草次酸,且糖基转移酶ugt73c11和unigene14953最适ph为7.0,糖基转移酶ugt73c5、ugt73c6、unigene20323最适ph为8.0。
实施例8:酶催化反应最适温度
将适度稀释糖基转移酶ugt73c11、ugt73c5、ugt73c6、unigene14953和unigene20323的粗酶液置于ph7.0缓冲液中,每个反应体系取100μl粗酶液,加入0.1μm甘草次酸和0.1μm尿苷二磷酸葡萄糖。分别置于25℃、30℃、35℃、40℃45℃、50℃和55℃等温度下,反应2h后进行酶活测定,研究重组酶的最适温度。由图6可知,重组酶在25-55℃之间均能合成3-o-葡萄糖基甘草次酸,且糖基转移酶ugt73c11、ugt73c5、ugt73c6和unigene14953最适温度为40℃,糖基转移酶unigene20323最适温度为45℃。
实施例9:糖基转移酶关键催化氨基酸位点突变验证
通过与已解析晶体结构的糖基转移酶的氨基酸序列对比发现,糖基转移酶ugt73c11的关键催化位点可能为24位的组氨酸和129位的天冬氨酸。通过pcr的方法,以pet28a-ugt73c11重组质粒为模板,将糖基转移酶ugt73c11的24位组氨酸和129位天冬氨酸分别突变为丙氨酸。所用引物为:
11-24f:5’>gctcagggtgctatgatcccgatggttgacatcgctcgt<3’如seqidno.29所示。
11-24r:5’>cgggatcatagcaccctgagccatgaacgggaacagaac<3’如seqidno.30所示。
11-129f:5’>atcatctctgctttctgcctgccgtacacctctaaaatc<3’如seqidno.31所示。
11-129r:5’>caggcagaaagcagagatgatgcaagacggctgcggaga<3’如seqidno.32所示。
pcr反应体系为:模板1μl,上下游引物各2μl,fastpfu(全式金生物公司)1μl,buffer10μl用双蒸水不足50μl。pcr反应条件:预变性95℃3min,变性95℃25s、退火58℃25s、延伸72℃3min30s,循环30次,72℃10min,4℃保存。
将pcr产物取8μl加入dpnⅰ1μl和酶切buffer1μl进行酶切2小时后,回收酶切产物,转化大肠杆菌bl21(de3)感受态细胞。涂布于含有100mg/l卡那霉素的固体lb培养基。筛选突变成功的阳性克隆进行诱导表达方法和酶活检测。结果表明将糖基转移酶ugt73c11的24位组氨酸和129位的天冬氨酸任何一个位点突变后,均丧失催化甘草次酸产生3-o-葡萄糖基甘草次酸的功能。由此可知糖基转移酶ugt73c11的24位组氨酸和129位天冬氨酸为关键催化氨基酸位点,对糖基转移酶ugt73c11催化生产3-o-葡萄糖基甘草次酸十分重要。
同样方法可测得糖基转移酶ugt73c5、ugt73c6、unigene14953和unigene20323的关键催化氨基酸位点为:
糖基转移酶ugt73c5的第23位的组氨酸(h)第128位的天冬氨酸(d);
糖基转移酶ugt73c6的第24位的组氨酸(h)第129位的天冬氨酸(d);
糖基转移酶unigene14953的第21位的组氨酸(h)第116位的天冬氨酸(d);
糖基转移酶unigene20323的第20位的组氨酸(h)第125位的天冬氨酸(d)。
所用突变引物为:
5-23f:5’>gctcaaggcgctatgattcccatggttgatattg<3’如seqidno.33所示。
5-23r:5’>gggaatcatagcgccttgagccatgaaagggaagagaac<3’如seqidno.34所示。
5-128f:5’>ctaatttctgcttttttgtttgccttatacaagc<3’如seqidno.35所示。
5-128r:5’>caaacaaaaagcgaaattagacagcttggtcg<3’如seqidno.36所示。
6-24f:5’>gctcaaggcgctatgattcccatggttgatattgc<3’如seqidno.37所示。
6-24r:5’>gggaatcatagcgccttgagccatgaaagggaagag<3’如seqidno.38所示。
6-129f:5’>ctaatctctgctatgtgtttgtcgtatacaagc<3’如seqidno.39所示。
6-129r:5’>caaacacatagcagagattagacagcttggtcgcgg<3’如seqidno.40所示。
53-21f:5’>tagcagctggtgcgatgatccctctatgcgac<3’如seqidno.41所示。
53-21r:5’>accagctgctaagtatggaatgaag<3’如seqidno.42所示。
53-116f:5’>gactgcatcgtcgccgcgttcctattcccc<3’如seqidno.43所示。
53-116r:5’>ggcgacgatgcagtctggtgggtcc<3’如seqidno.44所示。
23-20f:5’>atggctcaaggagccatcatccccatg<3’如seqidno.45所示。
23-20r:5’>tccttgagccattagtggaaacaag<3’如seqidno.46所示。
23-125f:5’>tgcataatctctgccttttgcattcct<3’如seqidno.47所示。
23-125r:5’>agagattatgcaacttggttttgg<3’如seqidno.48所示。
序列表
<110>北京理工大学
<120>一种酶法合成3-o-葡萄糖基甘草次酸的方法
<130>1
<150>2017106542619
<151>2017-08-03
<160>48
<170>siposequencelisting1.0
<210>1
<211>1434
<212>dna
<213>甘草(glycyrrhizauralensis)
<400>1
atggacgttgctgaagaacagccactcaaaatttacttcattccatacttagcagctggt60
cacatgatccctctatgcgacatagccacactcttcgcctcacgtggccaccacgtgacc120
atcatcaccactccctccaacgcccaaaccctccgcgaatcccaccacttccgcgtccaa180
accatccaattcccctcccaagaagtgggcctccccgccggcgtccaaaacctcaccgcc240
gtcacgaacctcgacgactcctataagatctaccacgccaccatgcttctccgcaaacac300
atcgaggacttcgtggagcgggacccaccagactgcatcgtcgccgacttcctattcccc360
tgggtggatgacgtggcaaccaagcttcacatcccaagactcgtcttcaacggcttcacc420
ttatttaccatctgtgccatggaatcccacaaggcacaccctctcccagttgatgccgcc480
tcgggttcttttgtgattcccgatttccctcaccatgtcactatcaattcaacaccccca540
aagcgcaccaaggaattcgtagaccctctgctcacggaagcgttcaagagccacggcttc600
ctcatcaacagcttcgtggagctcgacggagaagagtgcgtcgagcactacgagagaatc660
accggtggtcacaaggcttggcatcttggccctgcctttctcgttcacaggaccgctcaa720
gataggggagagaagagcgtggtgagcgcgcaggagtgcctgagttggctcgactcgaag780
cgagacaactcagtgctctacatatgctttggaaccatttgctatttcccagacaagcag840
ctttacgagatcgcaagcgcgattgaagcgtcgggtcacgaattcatatgggttgttccc900
gagaagagagggaatgatgatgagagcgaggaggagaaagaaaagtggctgccaaaggga960
tttgaagagaggaataatggaaagaaggggatgattataagggggtgggccccgcaggtg1020
gcgatcctgggccaccctgctgtgggcgggtttctaacgcattgcgggtggaactccacc1080
gtggaggccgttagcgcgggggttccgatgataacgtggccggtacatagcgatcaatac1140
ttcaacgagaagctgataactcaggtgagggggattggggtggaggtgggtgcggaggag1200
tggatcgtcactgcatttcgggagacggagaagctggtgggaagggatcgcatagagagg1260
gctgtaaggagggtgatggacggtggtgatgaggcggtacagatcagacggcgcgctcga1320
gagcttggggaaatggctagacaagctgttcaggaagggggctcgtctcacagtaatttg1380
acggccttgattaatgatcttaagcgatggagagactctaagcagcttaactaa1434
<210>2
<211>477
<212>prt
<213>甘草(glycyrrhizauralensis)
<400>2
metaspvalalaglugluglnproleulysiletyrpheileprotyr
151015
leualaalaglyhismetileproleucysaspilealathrleuphe
202530
alaserargglyhishisvalthrileilethrthrproserasnala
354045
glnthrleuarggluserhishispheargvalglnthrileglnphe
505560
proserglngluvalglyleuproalaglyvalglnasnleuthrala
65707580
valthrasnleuaspaspsertyrlysiletyrhisalathrmetleu
859095
leuarglyshisilegluaspphevalgluargaspproproaspcys
100105110
ilevalalaasppheleupheprotrpvalaspaspvalalathrlys
115120125
leuhisileproargleuvalpheasnglyphethrleuphethrile
130135140
cysalametgluserhislysalahisproleuprovalaspalaala
145150155160
serglyserphevalileproasppheprohishisvalthrileasn
165170175
serthrproprolysargthrlysgluphevalaspproleuleuthr
180185190
glualaphelysserhisglypheleuileasnserphevalgluleu
195200205
aspglygluglucysvalgluhistyrgluargilethrglyglyhis
210215220
lysalatrphisleuglyproalapheleuvalhisargthralagln
225230235240
aspargglyglulysservalvalseralaglnglucysleusertrp
245250255
leuaspserlysargaspasnservalleutyrilecyspheglythr
260265270
ilecystyrpheproasplysglnleutyrgluilealaseralaile
275280285
glualaserglyhisglupheiletrpvalvalproglulysarggly
290295300
asnaspaspgluserglugluglulysglulystrpleuprolysgly
305310315320
pheglugluargasnasnglylyslysglymetileileargglytrp
325330335
alaproglnvalalaileleuglyhisproalavalglyglypheleu
340345350
thrhiscysglytrpasnserthrvalglualavalseralaglyval
355360365
prometilethrtrpprovalhisseraspglntyrpheasnglulys
370375380
leuilethrglnvalargglyileglyvalgluvalglyalagluglu
385390395400
trpilevalthralaphearggluthrglulysleuvalglyargasp
405410415
argilegluargalavalargargvalmetaspglyglyaspgluala
420425430
valglnileargargargalaarggluleuglyglumetalaarggln
435440445
alavalglngluglyglyserserhisserasnleuthralaleuile
450455460
asnaspleulysargtrpargaspserlysglnleuasn
465470475
<210>3
<211>1470
<212>dna
<213>甘草(glycyrrhizauralensis)
<400>3
atggttttccaagcaaaccaacctcacttcgtcttgtttccactaatggctcaaggacac60
atcatccccatgatagacattgcaaggctcttagcacagcgtggtgctattgttaccata120
ttcactaccccaaaaaatgcatctcgtttcacctcagttctttctcgtgctgtttcctct180
ggcctccaaatccgactagtacatctccatttcccatcaaaagaagcaggactacctgaa240
gggtgtgaaaatcttgacatggtagcatcacatgacatgatatgcaatatcttccaagca300
attaggatgctccaaaagcaagcagaagaattgtttgagacactcacaccaaaaccaagt360
tgcataatctctgacttttgcattccttggactattcaagtagctgaaaagcaccacatt420
ccaaggatttctttccatggattctcttgcttctgcctccactgcatgctcaagatacac480
acttcaaaggttcttgaaggcatcacttcagaatcagagtacttcactgttcctggcata540
cctgaccaaattcaggttaccaaacagcaggtacctggaccaatgatagatgaaatgaag600
gaatttggggagcagatgcgtgatgctgagataaggtcatatggtgtaattatcaacact660
tttgaagagttggagaaagcatatgttaatgattacaagaaggaaagaaatggcaaggtt720
tggtgcattggccctgtttcactctgtaacaaagatgggttggataaggctcaaagaggc780
aacaaggcctcaattagtgaacaccattgcttggagtggctggatttgcagcagcccaat840
tctgtgatctatgtttgtcttggaagcttgtgcaatttaactcctccacaacttatggag900
ttggctttgggcttggaagccacaaaaaggccattcatttgggttattagggaaggaaat960
aagtttgaggagttggaaaagtggattagtgaagaagggtttgaggaaaggatcaagggg1020
agaggccttataattaggggttgggctccacaggtgttaatattatcacacccttccatt1080
gggggattcttaacacattgtggttggaactcaacacttgaaggggtaaccgctggggtc1140
ccaatggttacttggccactatttgctgatcagtttttgaatgagaagcttgttactcaa1200
gtgttgaggattggagtgagccttggggtagacgttccattgaagtggggagaagaagag1260
aaggttggtgttcaggtgaagaaggaaggtattgagaaggcaatatgcatggtgatggat1320
gagggagaggaaagtaaagagagaagagaaagggccaaggaactcagtgagatggcaaag1380
agagcagttgaaaaagatggatcttctcatcttaatatgacaatgcttatccaagacatt1440
atgcaacaatcaagtagtaaagttgaaact1470
<210>4
<211>490
<212>prt
<213>甘草(glycyrrhizauralensis)
<400>4
metvalpheglnalaasnglnprohisphevalleupheproleumet
151015
alaglnglyhisileileprometileaspilealaargleuleuala
202530
glnargglyalailevalthrilephethrthrprolysasnalaser
354045
argphethrservalleuserargalavalserserglyleuglnile
505560
argleuvalhisleuhispheproserlysglualaglyleuproglu
65707580
glycysgluasnleuaspmetvalalaserhisaspmetilecysasn
859095
ilepheglnalaileargmetleuglnlysglnalaglugluleuphe
100105110
gluthrleuthrprolysprosercysileileseraspphecysile
115120125
protrpthrileglnvalalaglulyshishisileproargileser
130135140
phehisglyphesercysphecysleuhiscysmetleulysilehis
145150155160
thrserlysvalleugluglyilethrsergluserglutyrphethr
165170175
valproglyileproaspglnileglnvalthrlysglnglnvalpro
180185190
glyprometileaspglumetlysglupheglygluglnmetargasp
195200205
alagluileargsertyrglyvalileileasnthrpheglugluleu
210215220
glulysalatyrvalasnasptyrlyslysgluargasnglylysval
225230235240
trpcysileglyprovalserleucysasnlysaspglyleuasplys
245250255
alaglnargglyasnlysalaserilesergluhishiscysleuglu
260265270
trpleuaspleuglnglnproasnservaliletyrvalcysleugly
275280285
serleucysasnleuthrproproglnleumetgluleualaleugly
290295300
leuglualathrlysargpropheiletrpvalilearggluglyasn
305310315320
lyspheglugluleuglulystrpileserglugluglyphegluglu
325330335
argilelysglyargglyleuileileargglytrpalaproglnval
340345350
leuileleuserhisproserileglyglypheleuthrhiscysgly
355360365
trpasnserthrleugluglyvalthralaglyvalprometvalthr
370375380
trpproleuphealaaspglnpheleuasnglulysleuvalthrgln
385390395400
valleuargileglyvalserleuglyvalaspvalproleulystrp
405410415
glyglugluglulysvalglyvalglnvallyslysgluglyileglu
420425430
lysalailecysmetvalmetaspgluglyglugluserlysgluarg
435440445
arggluargalalysgluleuserglumetalalysargalavalglu
450455460
lysaspglyserserhisleuasnmetthrmetleuileglnaspile
465470475480
metglnglnserserserlysvalgluthr
485490
<210>5
<211>495
<212>prt
<213>欧洲山芥(barbareavulgaris)
<400>5
metvalsergluilethrhislyssertyrproleuhisphevalleu
151015
pheprophemetalaglnglyhismetileprometvalaspileala
202530
argleuleualaglnargglyvallysilethrilevalthrthrpro
354045
hisasnalaalaargphegluasnvalleuserargalailegluser
505560
glyleuproileserilevalglnvallysleuproserglngluala
65707580
glyleuprogluglyasngluthrpheaspserleuvalsermetglu
859095
leuleuvalprophephelysalavalasnmetleuglugluproval
100105110
glnlysleuphegluglumetserproglnprosercysileileser
115120125
aspphecysleuprotyrthrserlysilealalyslyspheasnile
130135140
prolysileleuphehisglymetcyscysphecysleuleucysmet
145150155160
hisvalleuarglysasnarggluileleugluasnleulysserasp
165170175
lysgluhisphevalvalprotyrpheproaspargvalgluphethr
180185190
argproglnvalprometalathrtyrvalproglyglutrphisglu
195200205
ilelysgluaspilevalglualaasplysthrsertyrglyvalile
210215220
valasnthrtyrglngluleugluproalatyralaasnasptyrlys
225230235240
glualaargserglylysalatrpthrileglyprovalserleucys
245250255
asnlysvalglyalaasplysalagluargglyasnlysalaaspile
260265270
aspglnaspglucysleulystrpleuaspserlysglugluglyser
275280285
valleutyrvalcysleuglyserilecysserleuproleusergln
290295300
leulysgluleuglyleuglyleuglugluserglnargpropheile
305310315320
trpvalvalargglytrpglulysasnlysgluleuleuglutrpphe
325330335
seraspserglypheglugluargvallysaspargglyleuleuile
340345350
lysglytrpserproglnmetleuileleualahishisservalgly
355360365
glypheleuthrhiscysglytrpasnserthrleugluglyilethr
370375380
serglyileproleuleuthrtrpproleupheglyaspglnphecys
385390395400
asnglnlysleuvalvalglnvalleulysvalglyvalseralagly
405410415
valglugluvalthrasntrpglyglugluglulysileglyvalleu
420425430
valasplysgluglyvallyslysalavalglugluleumetglyglu
435440445
seraspaspalalysgluargarglysargvallysgluleuglygln
450455460
leualaglnlysalavalglugluglyglyserserhisserasnile
465470475480
thrserleuleugluaspilemetglnleualaglnserasnasn
485490495
<210>6
<211>495
<212>prt
<213>拟南芥(arabidopsisthaliana)
<400>6
metvalsergluthrthrlysserserproleuhisphevalleuphe
151015
prophemetalaglnglyhismetileprometvalaspilealaarg
202530
leuleualaglnargglyvalileilethrilevalthrthrprohis
354045
asnalaalaargphelysasnvalleuasnargalaileglusergly
505560
leuproileasnleuvalglnvallyspheprotyrleuglualagly
65707580
leuglngluglyglngluasnileaspserleuaspthrmetgluarg
859095
metileprophephelysalavalasnpheleuglugluprovalgln
100105110
lysleuilegluglumetasnproargprosercysleuileserasp
115120125
phecysleuprotyrthrserlysilealalyslyspheasnilepro
130135140
lysileleuphehisglymetglycysphecysleuleucysmethis
145150155160
valleuarglysasnarggluileleuaspasnleulysserasplys
165170175
gluleuphethrvalproasppheproaspargvalgluphethrarg
180185190
thrglnvalprovalgluthrtyrvalproalaglyasptrplysasp
195200205
ilepheaspglymetvalglualaasngluthrsertyrglyvalile
210215220
valasnserpheglngluleugluproalatyralalysasptyrlys
225230235240
gluvalargserglylysalatrpthrileglyprovalserleucys
245250255
asnlysvalglyalaasplysalagluargglyasnlysseraspile
260265270
aspglnaspglucysleulystrpleuaspserlyslyshisglyser
275280285
valleutyrvalcysleuglyserilecysasnleuproleusergln
290295300
leulysgluleuglyleuglyleuglugluserglnargpropheile
305310315320
trpvalileargglytrpglulystyrlysgluleuvalglutrpphe
325330335
sergluserglyphegluaspargileglnaspargglyleuleuile
340345350
lysglytrpserproglnmetleuileleuserhisproservalgly
355360365
glypheleuthrhiscysglytrpasnserthrleugluglyilethr
370375380
alaglyleuproleuleuthrtrpproleuphealaaspglnphecys
385390395400
asnglulysleuvalvalgluvalleulysalaglyvalargsergly
405410415
valgluglnprometlystrpglyglugluglulysileglyvalleu
420425430
valasplysgluglyvallyslysalavalglugluleumetglyglu
435440445
seraspaspalalysgluargargargargalalysgluleuglyasp
450455460
seralahislysalavalglugluglyglyserserhisserasnile
465470475480
serpheleuleuglnaspilemetgluleualagluproasnasn
485490495
<210>7
<211>495
<212>prt
<213>拟南芥(arabidopsisthaliana)
<400>7
metalapheglulysasnasnglupropheproleuhisphevalleu
151015
pheprophemetalaglnglyhismetileprometvalaspileala
202530
argleuleualaglnargglyvalleuilethrilevalthrthrpro
354045
hisasnalaalaargphelysasnvalleuasnargalailegluser
505560
glyleuproileasnleuvalglnvallyspheprotyrglngluala
65707580
glyleuglngluglyglngluasnmetaspleuleuthrthrmetglu
859095
glnilethrserphephelysalavalasnleuleulysgluproval
100105110
glnasnleuilegluglumetserproargprosercysleuileser
115120125
aspmetcysleusertyrthrsergluilealalyslysphelysile
130135140
prolysileleuphehisglymetglycysphecysleuleucysval
145150155160
asnvalleuarglysasnarggluileleuaspasnleulysserasp
165170175
lysglutyrpheilevalprotyrpheproaspargvalgluphethr
180185190
argproglnvalprovalgluthrtyrvalproalaglytrplysglu
195200205
ileleugluaspmetvalglualaasplysthrsertyrglyvalile
210215220
valasnserpheglngluleugluproalatyralalysaspphelys
225230235240
glualaargserglylysalatrpthrileglyprovalserleucys
245250255
asnlysvalglyvalasplysalagluargglyasnlysseraspile
260265270
aspglnaspglucysleuglutrpleuaspserlysgluproglyser
275280285
valleutyrvalcysleuglyserilecysasnleuproleusergln
290295300
leuleugluleuglyleuglyleuglugluserglnargpropheile
305310315320
trpvalileargglytrpglulystyrlysgluleuvalglutrpphe
325330335
sergluserglyphegluaspargileglnaspargglyleuleuile
340345350
lysglytrpserproglnmetleuileleuserhisproservalgly
355360365
glypheleuthrhiscysglytrpasnserthrleugluglyilethr
370375380
alaglyleuprometleuthrtrpproleuphealaaspglnphecys
385390395400
asnglulysleuvalvalglnileleulysvalglyvalseralaglu
405410415
vallysgluvalmetlystrpglyglugluglulysileglyvalleu
420425430
valasplysgluglyvallyslysalavalglugluleumetglyglu
435440445
seraspaspalalysgluargargargargalalysgluleuglyglu
450455460
seralahislysalavalglugluglyglyserserhisserasnile
465470475480
thrpheleuleuglnaspilemetglnleualaglnserasnasn
485490495
<210>8
<211>1488
<212>dna
<213>人工序列(artificialsequence)
<400>8
atggtttctgaaatcacccacaaatcttacccgctgcacttcgttctgttcccgttcatg60
gctcagggtcacatgatcccgatggttgacatcgctcgtctgctggctcagcgtggtgtt120
aaaatcaccatcgttaccaccccgcacaacgctgctcgtttcgaaaacgttctgtctcgt180
gctatcgaatctggtctgccgatctctatcgttcaggttaaactgccgtctcaggaagct240
ggtctgccggaaggtaacgaaaccttcgactctctggtttctatggaactgctggttccg300
ttcttcaaagctgttaacatgctggaagaaccggttcagaaactgttcgaagaaatgtct360
ccgcagccgtcttgcatcatctctgacttctgcctgccgtacacctctaaaatcgctaaa420
aaattcaacatcccgaaaatcctgttccacggtatgtgctgcttctgcctgctgtgcatg480
cacgttctgcgtaaaaaccgtgaaatcctggaaaacctgaaatctgacaaagaacacttc540
gttgttccgtacttcccggaccgtgttgaatttacccgtccgcaggttccgatggctacc600
tacgttccgggtgaatggcacgaaatcaaagaagacatcgttgaagctgacaaaacctct660
tacggtgttatcgttaacacctaccaggaactggaaccggcttacgctaacgactacaaa720
gaagctcgttctggtaaagcttggactatcggcccggtaagcctgtgcaacaaagttggt780
gctgacaaagctgaacgtggtaacaaagctgacatcgaccaggacgaatgcctgaaatgg840
ctggactctaaagaagaaggttctgttctgtacgtttgcctgggttctatctgctctctg900
ccgctgtctcagctgaaagaactgggtctgggtctggaagaatctcagcgtccgttcatc960
tgggttgttcgtggttgggaaaaaaacaaagaactgctggaatggttctctgagtctggt1020
ttcgaagaacgtgttaaagaccgtggtctgctgatcaaaggttggtctccgcagatgctg1080
atcctggctcatcactctgttggtggcttcctgacccactgcggttggaactctaccctg1140
gaaggtatcacctctggtatcccgctgctgacctggccgctgttcggtgaccagttctgc1200
aaccagaaactggttgttcaggttctgaaagttggtgtttctgctggtgttgaagaagtt1260
accaactggggtgaagaagaaaaaatcggtgttctggttgacaaagaaggtgttaaaaaa1320
gctgttgaagaactgatgggtgaatctgacgacgctaaagaacgtcgtaaacgtgttaaa1380
gaactgggtcagctggctcagaaagctgttgaagaaggtggttcttctcactctaacatc1440
acctctctgctggaagacatcatgcagctggctcagtctaacaactaa1488
<210>9
<211>1488
<212>dna
<213>拟南芥(arabidopsisthaliana)
<400>9
atggtttccgaaacaaccaaatcttctccacttcactttgttctcttccctttcatggct60
caaggccacatgattcccatggttgatattgcaaggctcttggctcagcgtggtgtgatc120
ataacaattgtcacgacgcctcacaatgcagcgaggttcaagaatgtcctaaaccgtgcc180
attgagtctggcttgcccatcaacttagtgcaagtcaagtttccatatctagaagctggt240
ttgcaagaaggacaagagaatatcgattctcttgacacaatggagcggatgatacctttc300
tttaaagcggttaactttctcgaagaaccagtccagaagctcattgaagagatgaaccct360
cgaccaagctgtctaatttctgatttttgtttgccttatacaagcaaaatcgccaagaag420
ttcaatatcccaaagatcctcttccatggcatgggttgcttttgtcttctgtgtatgcat480
gttttacgcaagaaccgtgagatcttggacaatttaaagtcagataaggagcttttcact540
gttcctgattttcctgatagagttgaattcacaagaacgcaagttccggtagaaacatat600
gttccagctggagactggaaagatatctttgatggtatggtagaagcgaatgagacatct660
tatggtgtgatcgtcaactcatttcaagagctcgagcctgcttatgccaaagactacaag720
gaggtaaggtccggtaaagcatggaccattggacccgtttccttgtgcaacaaggtagga780
gccgacaaagcagagaggggaaacaaatcagacattgatcaagatgagtgccttaaatgg840
ctcgattctaagaaacatggctcggtgctttacgtttgtcttggaagtatctgtaatctt900
cctttgtctcaactcaaggagctgggactaggcctagaggaatcccaaagacctttcatt960
tgggtcataagaggttgggagaagtacaaagagttagttgagtggttctcggaaagcggc1020
tttgaagatagaatccaagatagaggacttctcatcaaaggatggtcccctcaaatgctt1080
atcctttcacatccatcagttggagggttcctaacacactgtggttggaactcgactctt1140
gaggggataactgctggtctaccgctacttacatggccgctattcgcagaccaattctgc1200
aatgagaaattggtcgttgaggtactaaaagccggtgtaagatccggggttgaacagcct1260
atgaaatggggagaagaggagaaaataggagtgttggtggataaagaaggagtgaagaag1320
gcagtggaagaattaatgggtgagagtgatgatgcaaaagagagaagaagaagagccaaa1380
gagcttggagattcagctcacaaggctgtggaagaaggaggctcttctcattctaacatc1440
tctttcttgctacaagacataatggaactggcagaacccaataattga1488
<210>10
<211>1488
<212>dna
<213>拟南芥(arabidopsisthaliana)
<400>10
atggctttcgaaaaaaacaacgaaccttttcctcttcactttgttctcttccctttcatg60
gctcaaggccacatgattcccatggttgatattgcaaggctcttggctcagcgaggtgtg120
cttataacaattgtcacgacgcctcacaatgcagcaaggttcaagaatgtcctaaaccgt180
gccattgagtctggtttgcccatcaacctagtgcaagtcaagtttccatatcaagaagct240
ggtctgcaagaaggacaagaaaatatggatttgcttaccacgatggagcagataacatct300
ttctttaaagcggttaacttactcaaagaaccagtccagaaccttattgaagagatgagc360
ccgcgaccaagctgtctaatctctgatatgtgtttgtcgtatacaagcgaaatcgccaag420
aagttcaaaataccaaagatcctcttccatggcatgggttgcttttgtcttctgtgtgtt480
aacgttctgcgcaagaaccgtgagatcttggacaatttaaagtctgataaggagtacttc540
attgttccttattttcctgatagagttgaattcacaagacctcaagttccggtggaaaca600
tatgttcctgcaggctggaaagagatcttggaggatatggtagaagcggataagacatct660
tatggtgttatagtcaactcatttcaagagctcgaacctgcgtatgccaaagacttcaag720
gaggcaaggtctggtaaagcatggaccattggacctgtttccttgtgcaacaaggtagga780
gtagacaaagcagagaggggaaacaaatcagatattgatcaagatgagtgccttgaatgg840
ctcgattctaaggaaccgggatctgtgctctacgtttgccttggaagtatttgtaatctt900
cctctgtctcagctccttgagctgggactaggcctagaggaatcccaaagacctttcatc960
tgggtcataagaggttgggagaaatacaaagagttagttgagtggttctcggaaagcggc1020
tttgaagatagaatccaagatagaggacttctcatcaaaggatggtcccctcaaatgctt1080
atcctttcacatccttctgttggagggttcttaacgcactgcggatggaactcgactctt1140
gaggggataactgctggtctaccaatgcttacatggccactatttgcagaccaattctgc1200
aacgagaaactggtcgtacaaatactaaaagtcggtgtaagtgccgaggttaaagaggtc1260
atgaaatggggagaagaagagaagataggagtgttggtggataaagaaggagtgaagaag1320
gcagtggaagaactaatgggtgagagtgatgatgcaaaagagagaagaagaagagccaaa1380
gagcttggagaatcagctcacaaggctgtggaagaaggaggctcctctcattctaatatc1440
actttcttgctacaagacataatgcaactagcacagtccaataattga1488
<210>11
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>11
atggacgttgctgaagaacagcc23
<210>12
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>12
ttagttaagctgcttagagtctctc25
<210>13
<211>23
<212>dna
<213>人工序列(artificialsequence)
<400>13
atggttttccaagcaaaccaacc23
<210>14
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>14
agtttcaactttactacttgattgt25
<210>15
<211>30
<212>dna
<213>人工序列(artificialsequence)
<400>15
atggtttccgaaacaaccaaatcttctcca30
<210>16
<211>28
<212>dna
<213>人工序列(artificialsequence)
<400>16
tcaattattgggttctgccagttccatt28
<210>17
<211>30
<212>dna
<213>人工序列(artificialsequence)
<400>17
atggctttcgaaaaaaacaacgaacctttt30
<210>18
<211>30
<212>dna
<213>人工序列(artificialsequence)
<400>18
tcaattattggactgtgctagttgcattat30
<210>19
<211>34
<212>dna
<213>人工序列(artificialsequence)
<400>19
ccggaattcatggtttctgaaatcacccacaaat34
<210>20
<211>37
<212>dna
<213>人工序列(artificialsequence)
<400>20
acgcgtcgacgttgttagactgagccagctgcatgat37
<210>21
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>21
cgcggatccatggtttccgaaacaaccaaatcttctcca39
<210>22
<211>34
<212>dna
<213>人工序列(artificialsequence)
<400>22
cgcggatccattattgggttctgccagttccatt34
<210>23
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>23
cgcggatccatggctttcgaaaaaaacaacgaacctttt39
<210>24
<211>37
<212>dna
<213>人工序列(artificialsequence)
<400>24
acgcgtcgacattattggactgtgctagttgcattat37
<210>25
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>25
cgcggatccatggacgttgctgaagaacagcc32
<210>26
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>26
acgcgtcgacgttaagctgcttagagtctctc32
<210>27
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>27
cgcggatccatggttttccaagcaaaccaacc32
<210>28
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>28
acgcgtcgacagtttcaactttactacttgattgt35
<210>29
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>29
gctcagggtgctatgatcccgatggttgacatcgctcgt39
<210>30
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>30
cgggatcatagcaccctgagccatgaacgggaacagaac39
<210>31
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>31
atcatctctgctttctgcctgccgtacacctctaaaatc39
<210>32
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>32
caggcagaaagcagagatgatgcaagacggctgcggaga39
<210>33
<211>34
<212>dna
<213>人工序列(artificialsequence)
<400>33
gctcaaggcgctatgattcccatggttgatattg34
<210>34
<211>39
<212>dna
<213>人工序列(artificialsequence)
<400>34
gggaatcatagcgccttgagccatgaaagggaagagaac39
<210>35
<211>34
<212>dna
<213>人工序列(artificialsequence)
<400>35
ctaatttctgcttttttgtttgccttatacaagc34
<210>36
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>36
caaacaaaaagcgaaattagacagcttggtcg32
<210>37
<211>35
<212>dna
<213>人工序列(artificialsequence)
<400>37
gctcaaggcgctatgattcccatggttgatattgc35
<210>38
<211>36
<212>dna
<213>人工序列(artificialsequence)
<400>38
gggaatcatagcgccttgagccatgaaagggaagag36
<210>39
<211>33
<212>dna
<213>人工序列(artificialsequence)
<400>39
ctaatctctgctatgtgtttgtcgtatacaagc33
<210>40
<211>36
<212>dna
<213>人工序列(artificialsequence)
<400>40
caaacacatagcagagattagacagcttggtcgcgg36
<210>41
<211>32
<212>dna
<213>人工序列(artificialsequence)
<400>41
tagcagctggtgcgatgatccctctatgcgac32
<210>42
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>42
accagctgctaagtatggaatgaag25
<210>43
<211>30
<212>dna
<213>人工序列(artificialsequence)
<400>43
gactgcatcgtcgccgcgttcctattcccc30
<210>44
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>44
ggcgacgatgcagtctggtgggtcc25
<210>45
<211>27
<212>dna
<213>人工序列(artificialsequence)
<400>45
atggctcaaggagccatcatccccatg27
<210>46
<211>25
<212>dna
<213>人工序列(artificialsequence)
<400>46
tccttgagccattagtggaaacaag25
<210>47
<211>27
<212>dna
<213>人工序列(artificialsequence)
<400>47
tgcataatctctgccttttgcattcct27
<210>48
<211>24
<212>dna
<213>人工序列(artificialsequence)
<400>48
agagattatgcaacttggttttgg24
- 还没有人留言评论。精彩留言会获得点赞!
- 一种乙酰氨基葡萄糖苷酶检测试剂、反应垫、其制备方法及试剂盒与流程
- 一种氨基葡萄糖‑6磷酸合成酶突变体的制作方法与工艺
- 海洋α‑环糊精葡萄糖基转移酶转化淀粉制备α‑环糊精的方法与流程
- 一种高效合成乙酰氨基葡萄糖的重组枯草芽孢杆菌的制作方法与工艺
- N‑乙酰‑D‑氨基葡萄糖及其药物可接受盐在制备治疗病毒性肝炎药物中的应用及药物的制作方法与工艺
- N‑乙酰‑D‑氨基葡萄糖在制备治疗脱发和乌发药物、保健品中的应用及药物的制作方法与工艺
- 提高乙酰氨基葡萄糖产量的重组枯草芽孢杆菌及其构建方法与流程
- 一种提高乙酰氨基葡萄糖产量的重组枯草芽孢杆菌及其构建方法与流程
- 高产乙酰氨基葡萄糖的重组枯草芽孢杆菌及其构建方法与流程
- 微生物发酵生产N‑乙酰‑D‑氨基葡萄糖和/或D‑氨基葡萄糖盐的方法与流程
- 一种氨基葡萄糖‑6磷酸合成酶突变体的制作方法与工艺
- 海洋α‑环糊精葡萄糖基转移酶转化淀粉制备α‑环糊精的方法与流程
- 一种高效合成乙酰氨基葡萄糖的重组枯草芽孢杆菌的制作方法与工艺
- N‑乙酰‑D‑氨基葡萄糖及其药物可接受盐在制备治疗病毒性肝炎药物中的应用及药物的制作方法与工艺
- N‑乙酰‑D‑氨基葡萄糖在制备治疗脱发和乌发药物、保健品中的应用及药物的制作方法与工艺
- 一种提高N‑乙酰氨基葡萄糖产量的发酵方法与流程
- 提高乙酰氨基葡萄糖产量的重组枯草芽孢杆菌及其构建方法与流程
- 一种提高乙酰氨基葡萄糖产量的重组枯草芽孢杆菌及其构建方法与流程
- 高产乙酰氨基葡萄糖的重组枯草芽孢杆菌及其构建方法与流程
- 微生物发酵生产N‑乙酰‑D‑氨基葡萄糖和/或D‑氨基葡萄糖盐的方法与流程